DNA-Spuren bezeugen das Kräftemessen zwischen Viren und
Werbung

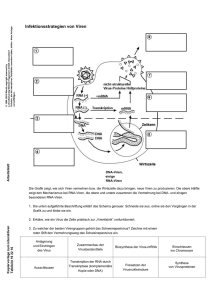
Jahrbuch 2010/2011 | Randau, Lennart | DNA-Spuren bezeugen das Kräftemessen zw ischen Viren und Bakterien DNA-Spuren bezeugen das Kräftemessen zwischen Viren und Bakterien Traces of DNA prove the test of strength between viruses and bacteria Randau, Lennart Max-Planck-Institut für terrestrische Mikrobiologie, Marburg Korrespondierender Autor E-Mail: [email protected] Zusammenfassung Dem bloßen Auge verborgen ereignet sich ein Kräftemessen einerseits zw ischen Bakterien und Archaeen und andererseits zw ischen Viren und anderen mobilen genetischen Elementen. Dieser Kampf hinterlässt Spuren in den jew eiligen Genomen und kann so in Anbetracht der Ko-Evolution beider Parteien nachvollzogen w erden. Eines der antiviralen Verteidigungsysteme von Bakterien, das CRISPR-System, beinhaltet Virenstücke im Genom, die die Geschichte der abgew ehrten Angriffe darlegen. Ein w eiterer Hinw eis ist die Trennung von transfer-RNA-Genen, die Viren nutzen, um sich in das W irtsgenom zu integrieren. Summary A nearly invisible battle rages on betw een Bacteria and Archaea on one side and viruses and other mobile elements on the other. This tug-of-w ar leaves its traces in the genomes of the involved parties and thus can be analyzed in respect of their co-evolution. One of the antiviral defense systems of Bacteria, the CRISPR system, contains pieces of viral DNA that provide direct insight into the history of previous viral attacks. Another indication of this battle is the disruption of transfer RNA genes used by viruses as attachment sites to facilitate their integration into the host genome. Einführung Unsere Erde w ird dominiert von den kleinsten Lebensformen, den Prokaryoten (Bakterien und Archaeen) mit einer beeindruckenden Population von geschätzten 4-6 x 10 30 -Zellen. Um eine Vorstellung solch einer immensen Zahl zu bekommen, w urde errechnet, dass die gleiche Anzahl an Pennies gestapelt eine Höhe von einer Billion Lichtjahren erreichen w ürde [1]. Selbst w enn man bedenkt, dass auf eine Zelle des menschlichen Körpers etw a zehn Bakterienzellen kommen, verblasst die Anzahl der Interaktionen von Bakterien mit Eukaryonten im Vergleich zum Kontakt von Bakterien mit einem anderen Partner, den Viren. So w urde gezeigt, dass Viren über zehnmal häufiger auf der Erde vorkommen als Prokaryoten und komplexe, sow ohl nützliche als auch schädliche Interaktionen mit Bakterien © 2011 Max-Planck-Gesellschaft w w w .mpg.de 1/6 Jahrbuch 2010/2011 | Randau, Lennart | DNA-Spuren bezeugen das Kräftemessen zw ischen Viren und Bakterien etabliert haben. Die Infektion durch ein Virus mit einem lytischen Vermehrungszyklus führt immer zur Lyse, also zum Tod des W irtsbakteriums. Die Entw icklung von verschiedenen raffinierten Abw ehrmechanismen gegen Viren bew eist die anhaltende Gefahr, die von diesen mobilen genetischen Elementen für Bakterien ausgeht. Die w ohl bekanntesten Abw ehrmechanismen sind die drei Restriktions-Modifikationssysteme, bei denen spezielle Restriktionsenzyme des Bakteriums die eindringende Virus-DNA erkennen und zerschneiden, w ohingegen die eigene DNA durch Methylierung modifiziert und geschützt w ird. Im Jahr 2007 w urde ein w eiteres Abw ehrsystem entdeckt, nämlich die antivirale Funktion der CRISPR- Systeme, die uns beim Blick in ein W irtsgenom einen faszinierenden Einblick in die Geschichte der Virenangriffe bietet. CRISPR/Cas – ein Immunsystem der Bakterien und Archaeen CRISPR-Elemente w urden zuerst in den späten 80er-Jahren als sich w iederholende kurze und unterbrochene Genomsequenzen im Modellbakterium Escherichia coli beschrieben [2]. Später w urde erkannt, dass solche Elemente in ungefähr 40% aller Bakterien als auch in fast allen Archaeen vorkommen und dass ein Genom mehrere dieser Elemente enthalten kann. Der Begriff CRISPR w urde eingeführt als Abkürzung für Clustered Regularly Interspaced Sh ort Palindromic Repeats (Cluster von kurzen, palindromischen, sich w iederholenden Sequenzen in gleichmäßigem Abstand), um die Eigenschaften dieser Elemente zu verdeutlichen. CRISPRElemente sind gekennzeichnet durch sich w iederholende Sequenzen mit einer Länge zw ischen 24 und 48 Basenpaaren (repeats), die von individuellen Sequenzen ähnlicher Länge (spacers) unterbrochen sind (Abb. 1). Die Anzahl der spacer-Einheiten variiert zw ischen ein bis zw ei und mehreren hundert in verschiedenen CRISPRElementen. Selbst sehr ähnliche Bakterienstämme können anhand der An-und Abw esenheit verschiedener CRISPR-Elemente unterschieden w erden. A bb. 1: Aufba u e ine s C R ISP R /C AS C luste rs. Ein C R ISP R C luste r ist im Ge nom a ls sich wie de rhole nde Se que nz a n ide ntische n re pe a ts und individue lle n Spa ce rse que nze n e rk e nnba r. Die Le a de rse que nz be inha lte t ve rm utlich P rom otore le m e nte . Die P roze ssie rung de r C R ISP R C luste r und die Abwe hr von Vire n we rde n durch C AS P rote ine k oordinie rt und a usge führt. Be i de n Spa ce rse que nze n ha nde lt e s sich um Ge nom bruchstück e von a bge we hrte n Vire n; die se ge be n e ine n historische n Einblick in die Ge schichte de r Inte ra k tione n de s W irts m it e ine r Vie lza hl a n Vire n und a nde re n m obile n Ele m e nte n. © Ma x -P la nck -Institut für te rre strische Mik robiologie /R a nda u; Vire na bbildunge n m it fre undliche r Ge ne hm igung von R oss B. Inm a n Ein erstes Anzeichen für eine mögliche Funktion dieser mysteriösen CRISPR-Elemente ergab in 2005 die © 2011 Max-Planck-Gesellschaft w w w .mpg.de 2/6 Jahrbuch 2010/2011 | Randau, Lennart | DNA-Spuren bezeugen das Kräftemessen zw ischen Viren und Bakterien Analyse von Spacersequenzen, die zeigte, dass diese Module in 124 Streptococcus thermophilus Stämmen Homologien zu Sequenzen von Bakteriophagen (77%), Plasmiden (16%), aber auch dem W irtsgenom (7%) aufw iesen [3]. Ein Durchbruch der Forschung kam im Jahr 2007, als Horvath and Barrango zeigen konnten, dass eine Spacersequenz im CRISPR-Element den W irt resistent gegen eine Infektion mit einem Virus mit übereinstimmender Sequenz im Genom macht [4]. Die Idee von CRISPR als ein generelles bakterielles Immunsystem w ar geboren. Weitere Arbeiten konnten zeigen, dass CRISPR auch die Konjugation von Plasmiden, die beispielsw eise Antibiotika-Resistenzen in klinischen Isolaten verbreiten, verhindert [5]. Die CRISPR-Funktion w urde auch in Archaeen identifiziert, die sogar eine größere Varibilität an CRISPR Systemen aufw eisen [6]. So können hyperthermophile Methanocaldococci über zw anzig verschiedene CRISPR-Elemente aufw eisen, die etw a 1% des gesamten Genomes ausmachen. Mechanismus des CRISPR-Systems W ie funktioniert ein CRISPR-System als antiviraler Verteidigungsmechanismus? In den letzten Jahren w urden große Fortschritte gemacht, um erste Hinw eise zur Funktion von CRISPR-Systemen zu erhalten. Eine erste w ichtige Entdeckung w ar das Vorhandensein von Clustern, bestehend aus konservierten Genen, die oftmals direkt neben den CRISPR-repeats lokalisiert w aren. Diese Gene kodieren Proteine, die CAS getauft w urde, w as fü r CRISP R associated sequences steht. Daher w erden CRISPR- Elemente oft vereinheitlicht als CRISPR/CasSysteme beschrieben. Die Annotation und Unterscheidung der Cas-Proteine erw eist sich allerdings als schw ierig, da oftmals nur eine geringe Ähnlichkeit auf der Sequenzebene festzustellen ist. Bislang w urden 45 verschiedene CAS-Proteinfamilien postuliert [7], die sich eventuell w eiter unterteilen lassen [8]. Mindestens sieben deutlich zu unterscheidende CAS-Protein-Subtypen w urden identifiziert, w as die Vielfalt der Funktionen und W irkungsw eisen der CRISPR/CAS-Systeme offenbart. Der Mechanismus der Immunität durch CRISPR/CAS-Systeme muss zumindest zw ei grundlegende Schritte beinhalten, die in der Regel als Adaptation und Interferenz bezeichnet w erden: i.) Adaptation meint die Erkennung des fremden, attackierenden Virusgenoms. Hierbei w ird ein Stück der VirenDNA/RNA (der protospacer) angegriffen und als neuer spacer am 5‘ Ende des W irts-CRISPR-Clusters eingebaut. Der Mechanismus des spacer-Einbaus ist noch unbekannt. Die Ausw ahl der protospacer befolgt nur w enige Regeln und scheint ansonsten w illkürlich. Zum einen darf ein protospacer nicht auch noch mit Teilen der CRISPR-repeat-Sequenz überlappen; dieser Mechanismus verhindert, dass der spacer nachfolgend im CRISPRCluster des W irtsgenoms nicht selbst als Ziel erkannt und attackiert w ird. Zum anderen w ird eine kurze Sequenz von zw ei bis drei dem protospacer folgenden Basen benötigt, um diesen als solchen auszuw eisen. ii.) Sobald der neue spacer im CRISPR-Cluster eingebaut ist, kann er zur Interferenz, also zur Abw ehr neuer Attacken des Viruses, aus dem er ursprünglich stammt, benutzt w erden. Dazu w ird das CRISPR-Cluster transkribiert und eine lange CRISPR-RNA hergestellt. Diese w ird von CAS-Proteinkomplexen in kleinere CRISPRRNAs (crRNAs) prozessiert. Die crRNAs binden anschließend durch Basenkomplementarität an die angreifende Virus-DNA (oder Virus-RNA, je nach Virustyp) und veranlassen deren Zerstörung durch einen zw eiten CASProtein- Komplex. In letzter Zeit w urden Erfolge erzielt, um Details der Funktionsw eise der verschiedenen CRISPR/Cas-Systeme auszuarbeiten. Zum Beispiel ist die Generierung von crRNA in verschiedenen Systemen inzw ischen schon gut erforscht. Andere Bereiche, w ie zum Beispiel der Einbau von spacern, der Mechanismus des Angriffs der Virengenome oder die Evolution und Verbreitung von CRISPR-Systemen, sind noch größtenteils unerforscht und sind im Begriff, ein faszinierendes und neuartiges Forschungsgebiet zu eröffnen. © 2011 Max-Planck-Gesellschaft w w w .mpg.de 3/6 Jahrbuch 2010/2011 | Randau, Lennart | DNA-Spuren bezeugen das Kräftemessen zw ischen Viren und Bakterien Eine w eitere interessante Fragestellung betrifft den Einbau von Spacersequenzen, die keine Übereinstimmung mit Viren oder Plasmid-DNA haben, sondern derart entw orfen w erden können, um experimentell beliebige Reporter- oder W irts-DNA zu attackieren. Damit könnte ein CRISPR/CAS-System eventuell als Mechanismus umgew andelt w erden, um gezielt Gene in Bakterien und Archaeen auszuschalten, w as den bekannten RNAInterferenz (RNAi)-Methoden in Eukaryoten ähneln w ürde. Selbst in den natürlich vorkommenden spacern finden sich Sequenzen des W irtes und es w ird vermutet, dass zum Beispiel CRISPR-Fragmente, Mutationen in CAS-Proteinen oder repeat Sequenzen die Spuren verhinderter Auto-Immunitätsreaktionen darstellen. Transfer RNA-Gene als Angriffspunkte von Viren Weitere vermutete Spuren der Ko-Evolution von Viren und Archaeen finden sich in den Genen für tRNAs. Diese kleinen RNAs übersetzen den genetischen Code in die entsprechende Aminosäure im Verlauf der ribosomalen Proteinbiosynthese. Damit sie ihre w ichtige Funktion ausüben können, müssen die Moleküle zw ei Bedingungen erfüllen. Einerseits müssen sie sich in eine L-förmige Tertiärstruktur falten, um im Ribosom w irken zu können. Andererseits müssen sie bestimmte Sequenz- und Strukurmerkmale aufw eisen, die ihre Spezifizität w ährend der Aminosäure-Beladung bestimmen. Zusammengenommen bedingt dies, dass eine Zelle nur sehr w enige Mutationen in solch w ichtigen RNAs zulassen kann. Dieses w ird in Archaeen von Viren ausgenutzt, die in den meisten Fällen große Teile der tRNA-Gene binden, um sich ins W irtsgenom zu integrieren. Dabei zerteilt das Virus das tRNA-Gen und rekonstituiert dieses nach erfolgreicher Integration. A bb. 2: Be ispie le von unte rbroche ne n tR NA Mole k üle n. Die m e iste n tR NAs fa lte n sich in de r Se k undä rstruk tur a ls k le e bla ttförm ige Mole k üle . In de n le tzte n Ja hre n wurde n m e hre re unte rschie dlich ze rstück e lte tR NA Ge ne in Archa e e n e ntde ck t, de re n tR NA Vorlä ufe rtra nsk ripte vom Splicingm e cha nism us de r Ze lle zum Erha lt funk tione lle r tR NA zusa m m e nge se tzt we rde n m üsse n. Die folge nde n Struk ture n k onnte n ide ntifizie rt we rde n: funk tione lle tR NA, tR NA m it Intron, ge te ilte tR NA und pe rm utie rte tR NA. Die zu e ntfe rne nde n Se que nza bschnitte sind in R ot und Grün m a rk ie rt. © Ma x -P la nck -Institut für te rre strische Mik robiologie /R a nda u Es w urde postuliert, dass diese Integration und das Entfernen von Viren an tRNA- Genen Spuren hinterlässt, die sich als Vorteil in der Evolution erw eisen können, falls damit eine Bindestelle des Viruses im tRNA-Gen zerstört w urde [9]. Basis dieser Hypothese ist die Entdeckung von mehreren, unterschiedlich zerstückelten tRNA- Genen in Archaeen (Abb. 2). Ein normales, durchgängiges tRNA-Gen misst im Durchschnitt 76 Basen. Dennoch w erden oft tRNA-Gene gefunden, die kurze Intronsequenzen beinhalten. Dabei kann es sogar vorkommen, dass ein tRNA-Gen mehrere Introns gleichzeitig enthält. Eine andere Art und Weise, um tRNAGene zu trennen, w urde zuerst in dem Archaeon Nanoarchaeum equitans beschrieben. Hier w erden sechs tRNA-Moleküle jew eils von zw ei einzeln hergestellten Stücken in trans zusammengefügt [10]. Interessanterw eise liegt eine dieser tRNA-Genhälften genau neben einem CRISPR-Cluster. Später w urden tRNA-Gene identifiziert, die auf drei individuelle tRNA-Genfragmente verteilt w urden. Schlussendlich fand man © 2011 Max-Planck-Gesellschaft w w w .mpg.de 4/6 Jahrbuch 2010/2011 | Randau, Lennart | DNA-Spuren bezeugen das Kräftemessen zw ischen Viren und Bakterien permutiertete RNA-Gene, bei denen die beiden Enden der Gene vertauscht w aren. Die Entstehung und Evolution dieser zerstückelten tRNA Gene w ird in den nächsten Jahren in Anbetracht ihrer „molekularen“ Ko-Evolution mit Viren untersucht. [1] W. B. Whitman, D. C. Coleman, W. J. Wiebe: Prokaryotes: the unseen majority. Proceedings of the National Academy of Sciences USA 95, 6578 - 6583 (1998). [2] A. Nakata, M. Amemura, K. Makino: Unusual nucleotide arrangement with repeated sequences in the Escherichia coli K-12 chromosome. Journal of Bacteriology 171, 3553 - 3556 (1989). [3] P. Horvath, D. A. Romero, A. C. Coute-Monvoisin, M. Richards, H. Deveau, S. Moineau, P. Boyaval, C. Fremaux, R. Barrangou: Diversity, activity, and evolution of CRISPR loci in Streptococcus therm ophilus. Journal of Bacteriology 190, 1401 - 1412 (2008). [4] R. Barrangou, C. Fremaux, H. Deveau, M. Richards, P. Boyaval, S. Moineau, D. A. Romero, P. Horvath: CRISPR provides acquired resistance against viruses in prokaryotes. Science 315, 1709 - 1712 (2007). [5] L. A. Marraffini, E .J. Sontheimer: CRISPR interference limits horizontal gene transfer in staphylococci by targeting DNA. Science 322, 1843-1845 (2008). [6] J. Carte, R. Wang, H. Li, R. M. Terns, M. P. Terns: Cas6 is an endoribonuclease that generates guide RNAs for invader defense in prokaryotes. Genes & Development 22, 3489-3496 (2008). [7] D. H. Haft, J. Selengut, E. F. Mongodin, K. E. Nelson: A guild of 45 CRISPR-associated (Cas) protein families and multiple CRISPR/Cas subtypes exist in prokaryotic genomes. PLoS Computational Biology 1, e60 (2005). [8] K. S. Makarova, N. V. Grishin, S. A. Shabalina, Y . I. Wolf, E. V. Koonin: A putative RNA-interference-based immune system in prokaryotes: computational analysis of the predicted enzymatic machinery, functional analogies with eukaryotic RNAi, and hypothetical mechanisms of action. Biology Direct 1, 7 (2006). [9] L. Randau, D. Söll: Transfer RNA genes in pieces. EMBO Reports 9, 623-628 (2008). [10] L. Randau, R. Münch, M. J. Hohn, D. Jahn, D. Söll: Nanoarchaeum equitans creates functional tRNAs from separate genes for their 5'- and 3'-halves. Nature 433, 537-541 (2005). © 2011 Max-Planck-Gesellschaft w w w .mpg.de 5/6 Jahrbuch 2010/2011 | Randau, Lennart | DNA-Spuren bezeugen das Kräftemessen zw ischen Viren und Bakterien © 2011 Max-Planck-Gesellschaft w w w .mpg.de 6/6