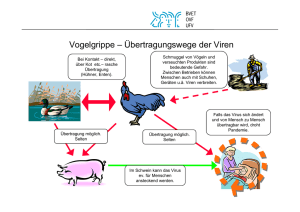
Dokument_39.
Werbung

Biochemische und molekularbiologische Charakterisierung des neuartigen Influenza-A-Virus Proteins PB1-F2 Der Naturwissenschaftlichen Fakultät der Friedrich-Alexander-Universität Erlangen-Nürnberg zur Erlangung des Doktorgrades Vorgelegt von David Mitzner aus Lichtenfels Als Dissertation genehmigt von der Naturwissenschaftlichen Fakultät der Universität Erlangen-Nürnberg Tag der mündlichen Prüfung: 12. März 2009 Vorsitzender der Prüfungskommision: Prof. Dr. Bänsch Erstberichterstatter: Prof. Dr. Ulrich Schubert Zweitberichterstatter: Prof. Dr. Andreas Burkovski Inhaltsverzeichnis Inhaltsverzeichnis 1. Zusammenfassung........................................................................................................ 1 1.1 Summary................................................................................................................... 2 2. Einleitung....................................................................................................................... 4 2.1 Die Familie der Orthomyxoviren............................................................................. 4 2.2 Epidemiologie und Tropismus des Influenza-A-Virus............................................ 5 2.3 Morphologie und Replikation des Influenza-A-Virus............................................. 7 2.4 Influenza und die virusinduzierte Apoptose............................................................ 10 2.5 Die influenzainduzierte Signaltransduktion und die Rolle der PKC-Aktivierung.. 14 2.6 PB1-F2, das 11. Influenzaprotein............................................................................ 17 3. Zielsetzung..................................................................................................................... 23 4. Material und Methoden................................................................................................ 24 4.1 Material.................................................................................................................... 24 4.1.1 Verbrauchsmaterial.......................................................................................... 24 4.1.2 Chemikalien und Reagenzien........................................................................... 24 4.1.3 Standard Puffer und Lösungen......................................................................... 25 4.1.4 Synthetische Peptide......................................................................................... 26 4.1.5 Antikörper......................................................................................................... 26 4.1.6 Plasmide und Oligonukleotide.......................................................................... 27 4.1.7 Bakterien und Bakterienkulturreagenzien......................................................... 27 4.1.8 Eukaryotische Zellen und Medien.................................................................... 28 4.1.9 Virus-Stocklösungen......................................................................................... 29 4.2 Methoden.................................................................................................................. 29 4.2.1 Standardmethoden............................................................................................. 29 4.2.2 Kultivierung eukaryotischer Zellen................................................................... 30 4.2.2.1 Inkubation und Passagieren von eukaryotischen Zellen................................ 30 4.2.2.2 Kultivierung von primären Zellen.................................................................. 30 4.2.2.3 Einfrieren und Auftauen von Zellen.............................................................. 31 4.2.2.4 Virusherstellung in Zellkultur........................................................................ 31 4.2.2.5 Virusinfektionen von Zellen........................................................................... 31 4.2.2.6 Plaque-Assay und Virustiter-Bestimmung.................................................... 32 4.2.3 Apoptosemessungen......................................................................................... 32 4.2.3.1 Annexin-V-Färbung zur FACS-Analyse....................................................... 32 Inhaltsverzeichnis 4.2.3.2 Caspase-3-Aktivitätsmessung........................................................................ 33 4.2.3.3 JC1-Färbung.................................................................................................. 33 4.2.4 Phosphorylierungsexperimente........................................................................ 33 4.2.4.1 Herstellung von S10-Extrakten..................................................................... 33 4.2.4.2 In-vitro-Phosphorylierung............................................................................. 34 4.2.4.3 In-vivo-Phosphorylierung.............................................................................. 34 4.2.4.4 Immunopräzipitation der radioaktiven Proben.............................................. 35 4.2.5 Chemisches Crosslinking.................................................................................. 35 5. Ergebnisse 5.1 Kinetik der PB1-F2 Expression in IAV infizierten Zellen.................................. 37 5.2 Untersuchung der pro-apoptotischen Wirkung von exogenem und endogenem PB1-F2 in Zellkultur............................................................................................... 38 5.2.1 Inkubation von Epithelzelllinien mit synthetischem PB1-F2 und Analyse mittels Annexin-V-Färbung............................................................................. 38 5.2.2 Exogenes sVpr, aber nicht sPB1-F2, induziert Apoptose in T-Lymphozyten. 40 5.2.3 Die Expression von endogenem PB1-F2 in 293T-Zellen hat keinen Einfluss auf die Caspase-3-Aktivität.............................................................................. 41 5.2.4 Exogenes sPB1-F2 hat keinen Einfluss auf die apoptotische Sensibilisierung verschiedener Zelllinien................................................................................... 43 5.2.5 PB1-F2 verstärkt die virusinduzierte Apoptose in humanen Monozyten......... 44 5.3 Das IAV-Protein PB1-F2 wird von der Proteinkinase C phosphoryliert.......... 45 5.3.1 PB1-F2 enthält mehrere potentielle Phosphorylierungsstellen mit PKC- und CK2-Konsensussequenzen............................................................................... 46 5.3.2 sPB1-F2 wird von der Protein-Kinase-C (PKC) in-vitro-phosphoryliert......... 47 5.3.3 PB1-F2 wird in transfizierten 293T-Zellen phosphoryliert.............................. 49 5.3.4 PB1-F2 wird an den PKC-Phosphorylierungsstellen Serin-35 und Threonin-27 in vitro phosphoryliert................................................................. 51 5.3.5 Mutationsanalysen zur Identifikation der relevanten Phosphorylierungsstellen von PB1-F2 in vivo............................................................................... 52 5.3.6 Die PB1-F2-Phosphorylierungsstelle Serin-35 ist in zahlreichen humanpathogenen Isolaten konserviert....................................................................... 54 5.3.7 Die Mutation der PB1-F2-Phosphorylierungsstellen resultiert in einer reduzierten Caspase-3-Aktivierung in primären humanen Monozyten............ 54 Inhaltsverzeichnis 5.4 Biochemische Charakterisierung der Oligomerisierung des PB1-F2-Proteins. 56 5.4.1 Das PB1-F2-Protein zeigt eine deutliche Tendenz zur Ausbildung von Oligomeren................................................................................................ 56 5.4.2 Das N-terminale PB-(1-40)- und C-terminale PB-(50-87)-Fragment von PB1-F2 besitzt die inhärente Fähigkeit zu oligomerisieren.............................. 57 5.4.3 Das Cystein in Position 42 ist durch die Ausbildung von Disulfidbrücken an der Oligomerisierung von PB1-F2 beteiligt................................................. 60 6. Diskussion 6.1 PB1-F2, ein viraler Pathogenitätsfaktor und die Frage nach den molekularen Mechanismen............................................................................................................ 62 6.2 Die Expression von PB1-F2 ist zeitlich reguliert..................................................... 64 6.3 Exogenes sPB1-F2 zeigt keine zytotoxischen Effekte in Zellkultur........................ 65 6.4 PB1-F2 ist ein Phosphoprotein und wird von der Proteinkinase C phosphoryliert. 67 6.5 PB1-F2 besitzt die intrinsische Eigenschaft, Oligomere auszubilden..................... 70 7. Abkürzungsverzeichnis................................................................................................ 73 8. Literaturverzeichnis...................................................................................................... 76 Zusammenfassung/Summary 1. Zusammenfassung Diese Arbeit beschäftigt sich mit der funktionellen und biochemischen Charakterisierung des im Jahre 2001 entdeckten 11. Influenza-A-Virus-(IAV)-Proteins PB1-F2. Vor kurzem wurde im Mausmodell gezeigt, dass PB1-F2 die Virulenz hochpathogener IAV-Isolate verstärkt. Weiterhin besitzt PB1-F2 funktionelle Ähnlichkeit zum pro-apoptotischen Vpr-Protein von HIV-1, weshalb zunächst untersucht wurde, ob extrazelluläres PB1-F2, ähnlich dem transduzierenden Vpr-Protein in der Lage ist, apoptotische Prozesse einzuleiten. Grundlage für diese Arbeitshypothese war die bekannte Tatsache, dass PB1-F2 in den Mitochondrien lokalisiert und pro-apoptotische Funktionen in einem noch nicht verstandenen Mechanismus vermittelt. In dieser Arbeit wurde gezeigt, dass weder extrazelluläres synthetisches (s)PB1-F2 noch intrazelluläres, durch Plasmid exprimiertes PB1-F2 ausreichend ist, um in verschiedenen Zelllinien Apoptose zu induzieren. Des Weiteren konnte hier gezeigt werden, dass nach der Infektion von primären humanen Monozyten ein apoptoseverstärkender Effekt in Gegenwart von PB1-F2 gemessen werden kann. Wurden dieselben Zellen mit einem PB1-F2-defizienten Virus infiziert, war die Apoptoseinduktion deutlich reduziert. Diese Befunde legen nahe, dass PB1-F2 nur im Kontext einer Virusinfektion pro-apoptotisch wirkt und dieser Effekt zellspezifisch ist, was in späteren Publikationen anderer Labore bestätigt wurde. Ein weiterer Schwerpunkt war die Untersuchung einer möglichen posttranslationalen Modifikation von PB1-F2. Es konnte hier erstmals gezeigt werden, dass PB1-F2 ein Phosphoprotein ist und direkt mit der Proteinkinase C (PKC) interagiert. Das virale Protein wurde von einem Extrakt aus verschiedenen konventionellen PKC-Isoformen sowie den Zellextrakten verschiedener Zelllinien effizient in vitro phosphoryliert. Die radioaktive 32 P- Markierung von transfizierten 293-T-Zellen und infizierten MDCK-Zellen ergab, dass PB1F2 in vivo phopshoryliert wird. Die in vitro und in vivo Phosphorylierung konnte in Gegenwart PKC-spezifischer Inhibitioren dosisabhängig inhibiert und durch den Aktivator PMA verstärkt werden. Es wurde mehrfach berichtet, dass die PKC nach einer IAV-Infektion aktiviert vorliegt, jedoch ist nur wenig über die Funktion dieser Aktivierung im Kontext der Virusreplikation bekannt. Als PB1-F2-relevante Phosphorylierungsstellen wurden in dieser Arbeit die Aminosäuren Threonin in Poistion 27 und Serin in Position 35 ermittelt, wobei die letztere in verschiedenen Isolaten konserviert ist, was eine Grundvoraussetzung für eine mögliche funktionelle Bedeutung der PB1-F2-Phosphorylierung wäre. Ein rekombinantes Virus, das für die Phosphorylierungsstellen in PB1-F2 mutiert wurde, zeigte nach der Infektion von primären Monozyten einen vergleichbaren Phänotyp wie eine Mutante, die durch gezielte Austauschmutationen nicht mehr in der Lage ist, PB1-F2 zu exprimieren. 1 Zusammenfassung/Summary Beide Virusmutanten waren im Vergleich zum Wildtyp-Virus in ihrer Fähigkeit eingeschränkt, effektiv Apoptose zu induzierten. Ob die Phosphorylierung von PB1-F2 auch für die kürzlich beschriebenen immunmodulatorischen Effekte des Proteins im Tiermodell von Bedeutung ist und in welchem Zusammenhang sie zur IAV-aktivierten, zellulären Signaltransduktion steht, bleibt noch Gegenstand zukünftiger Untersuchungen. PB1-F2 besitzt die inhärente Fähigkeit zu oligomerisieren. Dieses Phänomen wurde durch die Behandlung von sPB1-F2 mit chemischen Crosslinkern und anschließenden WesternblotAnalysen untersucht. Es zeigte sich, dass sowohl ein N-terminales als auch C-terminales Fragment von PB1-F2 Oligomere ausbildet, was mit dem in silico Befund übereinstimmt, dass das Protein je eine Oligomerisierungsdomäne im N- und C-terminalen Bereich besitzt, wobei die C-terminale Domäne ein deutlich größeres Potential zur Multimerisierung aufweist. Unter chemisch reduzierenden Bedingungen konnte gezeigt werden, dass das Cystein in Position 42 maßgeblich an der Ausbildung der dimeren Spezies von PB1-F2 durch Disulfidbindung beteiligt ist, wohingegen die PB1-F2-Multimerisierung ausschließlich auf die Integrität der Oligomerisierungsdomänen zurückgeführt werden kann. Über die funktionelle Relevanz der Oligomerisierung von PB1-F2 wurde bisher viel spekuliert. Die prominenteste Hypothese ist, dass PB1-F2 Membranporen ausbildet und möglicherweise zur Destabilisierung des mitochondrialen Membranpotentials beiträgt und damit funktionell der Gruppe der Viroporine zugeordnet werden kann. 1.1 Summary This study is focused on the functional and biochemical characterization of the novel 11th influenza A virus (IAV) protein PB1-F2. Recently, it was shown that PB1-F2 contributes to the increased virulence of highly pathogenic IAV strains and enhances the effects of secondary bacterial coinfection in mice. This results in severe pneumonia which is the major cause of influenza related mortality. PB1-F2 shares functional similarities to the pro-apoptotic Vpr protein of HIV-1. Initial experiments in this work are based on the hypothesis that extracellular synthetic (s)PB1-F2 might be able to induce apoptosis in cell culture, similar to the membrane transducing Vpr protein. PB1-F2 is predominantely located in the mitochondria of transfected or infected cells and mediates pro-apoptotic functions by a so far unknown mechanism. No cytotoxic effects were detected after incubation of different cell lines with extracellular PB1-F2. Also the plasmid mediated expression of PB1-F2 after transfection of 293T cells showed no influence on apoptosis induction. Additional experiments revealed that PB1-F2 is an enhancer of virus induced apoptosis after infection of primary human 2 Zusammenfassung/Summary monocytes, measured by caspase 3 acitivity. Therefore it was concluded that the pro-apoptotic effects of PB1-F2 are predominantly mediated after virus infection and in a cell-type-specific manner. Further studies shown in this work describe the discovery of PB1-F2 phopshorylation, which is a totally new finding in the field. PB1-F2 is phopshorylated in vitro by an extract containing the conventional isoforms of the protein kinase C (PKC) and by cellular S10 extract of different cell lines. 32P radiolabelling of transfected 293T cells and infected MDCK cells revealed that PB1-F2 is phosphorylated after expression in cell culture. The in vitro and in vivo phosphorylation of PB1-F2 is sensitive to inhibitors of PKC and could be increased by the PKC activator PMA. Several studies have shown that activation of the PKC occurs subsequent to influenza virus infection. However, the function of the PKC activation in the context of virus replication is unknown. The threonine in position 27 and the serine in position 35 have been identified as the relevant PKC phopshorylation sites of PB1-F2 with the latter being conserved in different influenza isolates which is a prerequisite for a general function of the phosphorylation phenomenon. A recombinant virus which is mutated for the PB1-F2 phopshorylation sites was impaired in its ability to induce apoptosis, similar to a mutant virus which is knocked out for PB1-F2 expression. If PB1-F2 phopshorylation is also important for the recently described immunomodulatory effects and pathogenicity remains to be investigated. PB1-F2 displays the inherent ability to undergo oligomerization. This phenomenon was characterized by the use of sPB1-F2 with chemical crosslinkers and western blot analysis. In silico analysis revealed that the protein displays two oligomerization domains in the C-terminus and a much weaker domain in the N-terminus, which is consistent with the finding that both, a N-terminal and a C-terminal fragment of PB1-F2 are able to form multimers, while the C-terminal fragment has a much higher propensity for oligomerization. Under chemically reducing conditions it was shown that the cystein in position 42 mediates the dimerization of PB1-F2 by disulfid-bridges whereas the protein multimerization depends mainly on the integrity of the oligomerization sites. There has been much speculation about the functional relevance of the oligomerization phenomenon. The most prominent hypothesis suggests that PB1-F2 oligomerization results in the formation of membrane-pores and therefore contributes to the destabilization of the mitochondrial membrane potential, suggesting that PB1-F2 mediates a viroporin-like function. 3 Einleitung 2. Einleitung 2.1 Die Familie der Orthomyxoviren Die Familie der Orthomyxoviren zeichnet sich durch ein einzelsträngiges RNA-Genom mit negativer Polarität aus, das linear segmentiert vorliegt, wodurch sie sich von anderen RNAViren deutlich abgrenzen und ein hohes Maß an genetischer Flexibilität besitzen. Die Bezeichnung leitet sich vom griechischen „myxa“ (Schleim) ab, da die Vertreter dieser Familie eine hohe Affinität zu Schleimhäuten besitzen. Orthomyxoviren werden in vier Gattungen unterteilt (Leahy, Dessens et al. 1997; Pringle 1998). Zu ihnen gehören, wie in Tabelle 1 dargestellt, die Influenza-Viren A, B und C, das Thogotovirus, zusammen mit dem Dhorivirus und das Isavirus (Infectious Salmon Anemia Virus), das jedoch keine eigene Gattung bildet (Klenk 1995; Falk, Namork et al. 1997; Regenmortel 2000). Die Aufteilung der Influenza-Viren in die Genera A, B und C erfolgt aufgrund der serologischen Unterschiede in ihrem Nukleoprotein (NP) bzw. Matrixprotein (M). Die Anzahl der RNASegmente variiert zwischen den verschiedenen Gattungen: acht Segmente bei Influenza A und B und dem Isavirus, sieben Segmente bei Influenza C und dem Dhorivirus und sechs für das Thogotovirus. Eine weitere Unterteilung erfolgt durch die Hüllproteine der Viren. Nur Influenza-A und -B-Viren besitzen die Oberflächenproteine Hämagglutinin (HA) und Neuraminidase (NA). Bei Influenza-C ist die NA durch ein glykosyliertes HämagglutininEsterase-Fusionsprotein (HEF) ersetzt (Herrler and Klenk 1991). Das Thogoto- und Dhorivirus haben nur ein einziges Glykoprotein auf der Oberfläche, welches bei anderen Influenza-Viren nicht zu finden ist (Morse, Marriott et al. 1992). Die Influenza-A-Viren werden je nach Antigenität ihrer HA- und NA-Proteine in mehrere Subtypen klassifiziert. Im Augenblick sind 16 HA (H1, H2, usw.) und 9 NA (N1, N2, usw.) antigene Subtypen beschrieben (Fouchier, Munster et al. 2005), für die Influenza-B und -C-Viren sind bisher keine Subtypen bekannt. Durch die WHO (World Health Organisation) wurde eine einheitliche Nomenklatur für Influenza-A-Viren eingeführt. Sie bezeichnet den Typ, den Ort der Isolierung, die Nummer des Isolates und das Jahr, in dem das Virus isoliert wurde, z.B. der Influenza-A-Virus (IAV) Stamm A/Puerto Rico/8/34 (H1N1). Der Krankheitsverlauf des Influenza-C-Virus ist beim Menschen von geringer Bedeutung, und auch das Influenza-B-Virus verursacht eher selten ernsthafte Erkrankungen (Chen and Holmes 2008). Einzig die Gattung der Influenza-A-Viren stellt eine alljährliche und globale Bedrohung dar, die neben extremen ökonomischen und gesundheitspolitischen Problemen auch die aktuelle Diskussion einer möglichen bevorstehenden Pandemie durch das Vogelgrippevirus entfacht hat (Korteweg and Gu 2008; Lee and Saif 2008). 4 Einleitung Gattung Wirte Influenza-A-Virus Mensch,Vogel, Segmentzahl Oberflächenproteine HA, NA Schwein, Pferd, 8 Robbe Influenza-B-Virus Mensch, Robbe Influenza-C-Virus Mensch, Schwein, 8 7 Hund HA, NA HEF Isavirus Lachs 8 HA, Esterase Thogotovirus Zecke, Rinder, 6 1 Glykoprotein Schafe, Nagetiere Tab. 1 Die Familie der Orthomyxoviren mit ihren natürlichen Wirten und taxonomischen Unterscheidungsmerkmalen. 2.2 Epidemiologie und Tropismus des Influenza-A-Virus Die Evolution humaner Influenza-A-Viren erfolgt durch zwei primäre Mechanismen (Webster, Bean et al. 1992; Wright 2001). Beim sogenannten „antigenic drift“ bilden sich in einem langsam fortschreitenden Prozeß von Punktmutationen subtile Varianten von aktuell zirkulierenden Viren. Diese Mutanten sind für die Influenza-A-Virus Epidemien verantwortlich, wie sie in den meisten Ländern jährlich vorkommen. Im Gegensatz dazu steht der „antigenic shift“, der sich auf den Austausch ganzer RNA-Segmente zwischen verschiedenen Influenza-A-Viren innerhalb eines Wirtes zurückführen lässt. Der primäre Wirt der Influenza-A-Viren sind Wasservögel, die ein riesiges, permanent präsentes und globales Reservoir an Influenzaviren darstellen (Webster, Bean et al. 1992; Webby and Webster 2001). Alle 16-HA und 9-NA Subtypen konnten bisher aus ihnen isoliert werden, wohingegen beim Menschen nur H1, H2, H3 und N1 sowie N2 nachgewiesen wurden (Webster, Bean et al. 1992). Dabei besteht die eher seltene Möglichkeit, dass es entweder zu einer direkten Übertragung einer aviären Variante auf den Menschen kommt, oder dass im sogenannten „genetic reassortment“ ein Austausch von Segmenten aktuell zirkulierender humaner Viren mit einem Vogelgrippevirus zur Bildung eines neuen, hochpathogenen und auf den Menschen übertragbaren Virus führt. Dieser Prozess wird als „reassortment“ bezeichnet und findet in einem Zwischenwirt, wie z.B. dem Schwein statt, das als „mixing vessel“ fungiert, in dem neue Viren mit heterogenen Oberflächenantigenen gebildet werden. Besonders hervorzuheben sind die vier großen Pandemien des vergangenen Jahrhunderts, bekannt als die „Asiatische Grippe“ von 1957, die „Hongkong Grippe“ von 1968 und die 5 Einleitung „Russische Grippe“ von 1977, mit jeweils einer Million Opfer weltweit (Cox and Subbarao 2000) und die berüchtigte „Spanische Grippe“ von 1918, die nach heutigen Schätzungen etwa 25% der damaligen Weltbevölkerung infiziert und zwischen 20 und 40 Millionen Menschen getötet hat (Taubenberger, Reid et al. 2000; Taubenberger, Reid et al. 2001). Es gilt inzwischen als wahrscheinlich, dass sich die Spanische Grippe auf einen aviären Ursprung zurückführen lässt (Taubenberger, Reid et al. 2005). Dabei wächst die Befürchtung, dass die Bildung solcher hochpathogener Viren jederzeit wieder erfolgen kann, wobei die größten Bedenken in der Mensch zu Mensch Übertragung eines reassortierten Vogelgrippevirus liegen, da sich in keiner humanen Population Antikörper gegen H5, H7 oder H9 befinden (Webby and Webster 2001) (Abb. 2.2). Eine entscheidende biologische Barriere hierfür ist der unterschiedliche Tropismus zwischen Vogelgrippeviren und humanen Viren. Zur Bindung an die Zelloberfläche nutzen InfluenzaViren Sialinsäure, welche über die Galactose mit Zuckerresten verknüpft ist. Aviäre Influenza-Viren binden bevorzugt an Sialylsäureoligosaccharide mit einer α2,3- galactosidischen Bindung, wie sie vor allem auf Zellen des Darmtraktes von Vögeln zu finden ist, wohingegen humane Influenza-Viren eine α2,6-Verknüpfung präferieren, eine Variante, die für tracheale Epithelzellen typisch ist (Suzuki, Ito et al. 2000; Wright 2001). Abb. 2.2 Weltkarte mit allen Ländern, in denen das H5N1 Virus nachgewiesen werden konnte. (Nach dem U.S. Department of Health and Human Services, www.hhs.gov). 6 Einleitung Jedoch befinden sich im menschlichen Respirationstrakt Bereiche von zilienbildenden Zellen, welche α2,3-verknüpfte Sialinsäurerezeptoren exponieren und ausreichend sind, um eine Vogelgrippevirus-Infektion zu ermöglichen (Matrosovich, Matrosovich et al. 2004). Die Tatsache, dass es bisher nur 385 belegte Fälle einer solchen Übertragung auf den Menschen gibt, verdeutlicht, dass es sich hier um ein eher seltenes Ereignis handelt. 2.3 Morphologie und Replikation des Influenza-A-Virus Das Influenza-Viruspartikel ist vielgestaltig (pleiomorph), da die Partikelgröße und -form stark variieren kann. Hauptsächlich lassen sich sphärische Formen mit einem Durchmesser von etwa 80-120 nm vorfinden (Abb. 2.3.1A), aber auch filamentöse Partikel mit einer Länge von bis zu 300 nm sind bekannt. Die Virushülle besteht aus einer Lipidmembran, die von Glykoproteinen durchsetzt ist. Bei diesen handelt es sich um vereinzelte OberflächenproteinCluster, die in einem HA/NA-Verhältnis von etwa 5:1 stehen. Die Innenseite der Hülle ist durch das Matrixprotein (M1) ausgekleidet und von einigen Ionenkanälen, bestehend aus dem Tetramer des M2-Proteins, durchsetzt. Das Genom des Influenza-A-Virus besteht aus einzelsträngiger RNA mit negativer Orientierung (-RNA). Die Genomgröße beträgt 13,5 Kilobasen (kB), welche sich auf acht Segmente, die viralen Ribonukleoproteinkomplexe (vRNP`s) aufteilen. Diese Komplexe sind zwischen 50 und 130 nm lang, besitzen eine helikale Symmetrie und bestehen aus Nukleoproteinen (NP’s) mit gebundener RNA und einem assoziierten RNA- Polymerasekomplex, der sich aus den „basischen“ viralen Polymerasen PB1 und PB2 sowie der „sauren“ PA-Untereinheit zusammensetzt (Abb. 2.3.1B). Jedes funktionsfähige Virusparitkel benötigt zur effizienten Infektion einen zellulären Rezeptor. Dieser wurde für Influenza bereits vor 50 Jahren als Sialinsäure beschrieben (Gottschalk 1959). Seitdem ist bekannt, dass das Virus über sein HA- Glykoprotein an die Sialinsäurereste der Zelloberfläche bindet (Abb. 2.3.2), wie sie auf zellulären Glykoproteinen oder Lipiden zu finden sind (Skehel and Wiley 2000). Als typische Wirtszelle der humanen Influenza gilt die Lungenepithelzelle des Respirationstraktes mit einer α2,6-verknüpften Sialinsäure auf der apikalen Plasmamembran (Baum and Paulson 1990). Die Aufnahme des Viruspartikels erfolgt durch rezeptorvermittelte Endozytose (Patterson, Oxford et al. 1979; Matlin, Reggio et al. 1981), wobei das HA-Protein auch als Fusionsprotein von Bedeutung ist (Skehel and Wiley 2000). Nach der Ausbildung eines sogenannten späten endosomalen Kompartimentes erfolgt die Freisetzung (uncoating) in das Zytoplasma (Bui, Whittaker et al. 7 Einleitung 1996). Diesem Prozess geht eine vorhergehende Ansäuerung des Viruspartikels voraus, welche über den M2-Ionenkanal vermittelt wird (Pinto, Holsinger et al. 1992). A B NP Abb. 2.3.1 Aufbauf des Influenza-A-Virions und RNP-Komplexes. (A) Das Influenza-A-Virus besitzt 11 Proteine, welche durch 8 einzelsträngige RNA-Segmente in negativer Orientierung kodiert werden und ist von einer Lipiddoppelschicht umhüllt, in welche die Hüllproteine eingelagert sind (Abb. nach Webster et al. 1992). Zu den Influenzaproteinen zählen die Neuraminidase (NA), Hämagglutinin (HA), der virale Polymerase-Komplex mit dem basischen Protein 1, 2 (PB1, PB2) und dem sauren Protein (PA), das RNA bindende Nukleoprotein (NP), Matrix 1 und 2 (M1, 2), die Nicht-Strukturproteine (NS 1, 2) und das akzessorische PB1-F2-Protein aus dem offenen Leserahmen 2 des PB1-Gens. (B) Modell der Ribonukleoproteinstruktur. Die einzelsträngige virale RNA (vRNA) umwickelt die NP-Monomere und bildet eine Haarnadelstruktur aus. Die 5’- und 3’-Enden bilden eine kurze doppelsträngige Region aus, welche an die heterotrimere RNA-Polymerase (PA, PB1, PB2) bindet (Abb. nach Portela und Digard, 2002). Dies ist auch der Angriffspunkt für Amantadin, eine antivirale Sustanz, welche den Ionenkanal und somit die Nukleokapsidfreisetzung blockiert (Bukrinskaya, Vorkunova et al. 1982; Martin and Helenius 1991). Durch den niedrigen pH-Wert ändert sich die Konformation der aminoterminalen Region des HA-Proteins, so dass die endosomale und virale Membran miteinander fusionieren. Die zunehmende Ansäuerung des Partikels führt zu einer erneuten Konformationsänderung des HA und löst die Interaktion zwischen den Nukleoproteinen und RNP-Partikeln mit den M1-Hüllstrukturproteinen, was die Voraussetzung für die Freisetzung der viralen RNA in das Zytoplasma ist (Bui, Whittaker et al. 1996). Die RNPs gelangen durch einen Mechanismus, der bisher nicht eindeutig geklärt ist, in den Zellkern, den Ort der viralen Transkription (Herz, Stavnezer et al. 1981). Voraussetzung hierfür ist die Passage des RNPs durch die Kernmembran. Für einen passiven 8 Einleitung Diffusionsprozess sind die Komplexe zu groß (Paine 1975). Alle Proteine des RNP, einschließlich der Polymeraseproteine besitzen eine NLS (nuclear localization sequence) (Nath and Nayak 1990; Nieto, de la Luna et al. 1994). Die aktive Aufnahme in den Kern erfolgt über das NP, welches hierfür an das Kernporenprotein Importin-α bindet, einer wichtigen Komponente des Kernimport-Systems (Gorlich, Prehn et al. 1994). Abb. 2.3.2 Der IAV-Replikationszyklus. Nach der rezeptorspezifischen Bindung des viralen HA an die Zelloberfläche (1) erfolgt die endozytotische Aufnahme des Viruspartikels (2) und die Freisetzung des Nukleokapsides in das Zytosol der Wirtszelle (3). Dieses wandert in den Kern, welcher der Ort der viralen RNA-Replikation ist (4). Die Translation der viralen Oberflächenproteine erfolgt in das endoplasmatische Retikulum (ER), und ein Teil der für die RNA-Replikation notwendigen Virusproteine gelangt wieder in den Kern (5). Am Ende der Replikation steht die Generierung und der Kernexport eines Ribonukleoproteinkomplexes (6), welcher zur Zelloberfläche gelangt und mit den viralen Oberflächenproteinen unter Ausbildung eines neuen Viruspartikels abgeschnürt wird (Abb. der ViroLogik GmbH Erlangen). Die virale RNA hat im Zellkern zwei wesentliche Funktionen: Sie dient als Matrize zur Synthese viraler mRNA und neuer genomischer RNA. Zu den früh translatierten Virusproteinen zählen PB1, PB2, PA, NP, NS1 und NS2, die nach der Synthese wieder in den 9 Einleitung Kern zurück gelangen. Im Kern erfolgt die Initiation der RNA-Synthese durch die virale RNA-abhängige RNA-Polymerase, die sich aus den PB1-, PB2- und PA-Proteinen zusammensetzt. Zur Replikation der viralen RNA (vRNA) wird zunächst copy-RNA (cRNA) synthetisiert, die einen Anteil von nur etwa 5-10% der gesamten viralen RNA ausmacht (Hay, Lomniczi et al. 1977; Herz, Stavnezer et al. 1981) und weder eine Cap-Struktur aufweist, noch polyadenyliert ist. Ein weiterer bedeutender Faktor der Replikation ist das NP. Es wird spekuliert, dass seine Bindung an vRNA den Übergang der viralen mRNA- zur cRNASynthese reguliert (Klumpp, Ruigrok et al. 1997). Nach der Synthese viraler RNA bilden sich neue RNPs, die sich aus den drei Untereinheiten des viralen Polymerasekomplexes und der einzelsträngigen v-RNA, die unspezifisch an NP gebunden ist, zusammensetzt (Huang, Palese et al. 1990). Nach dem Kernexport der RNPs assembliert das Influenza-A-Virus in Epithelzellen an der apikalen Plasmamembran (Bachi, Gerhard et al. 1969), wobei die viralen Proteine HA, NA und M2 unabhängig voneinander vom endoplasmatischen Retikulum über den Golgiapparat zur Zellmembran transportiert werden (Gottlieb, Gonzalez et al. 1986). Die HA- und NA- Glykoproteine werden zu cholesterinreichen Mikrodomänen der Zelloberfläche, den sogenannten „lipid rafts“, gesteuert (Barman and Nayak 2000), von denen aus die Viruspartikel assembliert werden (Scheiffele, Rietveld et al. 1999; Takeda, Leser et al. 2003). Ob der Transport der RNP-Komplexe und des viralen M1 zur Zellmembran ungerichtet (Patterson, Gross et al. 1988) oder, wie neuere Daten andeuten, gerichtet ist (Ali, Avalos et al. 2000), bleibt kontrovers. Das virale M1-Protein dient als Adaptermolekül zwischen der Zellmembran und dem RNP als auch zwischen dem RNP und dem zytosolischen Teil der viralen Glykoproteine HA, NA, M2 (Barman, Ali et al. 2001), und das so assoziierte neue Viruspartikel wird durch Abknospung von der Membran freigesetzt (Webster, Bean et al. 1992). 2.4 Influenza und die virusinduzierte Apoptose Die Untersuchung der Apoptoseinduktion durch das Influenza-Virus ist von zunehmender Bedeutung für das Verständnis der Mechanismen der viralen Pathogenität (Benedict, Norris et al. 2002; Yewdell and Garcia-Sastre 2002; Lowy 2003). Unter Apoptose versteht man eine biochemisch und morphologisch definierte Form des programmierten Zelltodes, welche von einer Zelle aktiv durchgeführt wird (Kerr, Wyllie et al. 1972) und für eine Vielzahl von Viruserkrankungen von Bedeutung ist (Razvi and Welsh 1995). Dabei können die komplexen und verzweigten apoptotischen Prozesse in eine mitochondriale (intrinsische) und eine Todesrezeptor-abhängige (extrinsische) Signalkaskade unterteilt werden (Abb. 2.4), welche beide in der Aktivierung der spezifischen Caspasen 10 Einleitung (Cystein Aspartasen) konvergieren (Cohen 1997). Apoptose-induzierende Caspasen werden hauptsächlich in Initiatorcaspasen, wie die Procaspasen-8 und -9, und in die Effektorcaspasen wie zum Beispiel Caspase-3, -6 und -7, unterteilt. Die Procaspasen dienen als Vermittler zwischen apoptotischen, zellulären Signalen und der proteolytischen Aktivierung der Effektorcaspasen. Sind letztere erst einmal aktiviert, erfolgt der gezielte und irreversible proteolytische Abbau von zellulären Proteinen und Strukturen sowie die Fragmentierung der Kern-DNA (Kroemer, Dallaporta et al. 1998; Thornberry and Lazebnik 1998). Es gibt eine Vielzahl biochemischer und morphologischer Apoptosemarker, welche in der Vergangenheit zur Detektion des IAV-induzierten Zelltodes verwendet wurden. Zu den wichtigsten biochemischen Markern zählen die Detektion von extrazellulär exponiertem Phosphatidylserin durch Annexin-V, die Messung des mitochondrialen Membranpotentials und einsetzender Depolarisation, die Freisetzung von Cytochrom-c aus dem mitochondrialen Membranzwischenraum und die spezifische Caspasen-Aktivierung, im Besonderen die der Caspasen-8 und -3 (Lowy 2003). Die Zeiosis, eine spezielle und apoptosetypische morphologische Erscheinung, die sich durch Zytoplasmaschrumpfung und Abschnürung kleiner membranumhüllter Bläschen (membrane blebbing) äußert, ist im Kontext einer IAVInfektion nur schwer und in bestimmten Zellen nachweisbar (Wyllie, Kerr et al. 1980; Lowy and Dimitrov 1997; Fujimoto, Takizawa et al. 1998). Apoptotische Prozesse werden durch Influenza-A- und -B-Viren induziert und können sowohl in Zellkultur als auch in vivo nachgewiesen werden (Fesq, Bacher et al. 1994; Hinshaw, Olsen et al. 1994; Mori, Komatsu et al. 1995; Ito, Kobayashi et al. 2002). Neben den Lungenepithelzellen wurde die IAVinduzierte Apoptose in verschiedenen Tiermodellen auch in Milz, Thymus, Leber, Nieren und sogar dem Gehirn festgestellt (Mori, Komatsu et al. 1995; Ito, Kobayashi et al. 2002; Lowy 2003). Auch in Zellen, welche die IAV-Replikation nicht produktiv unterstützen, z.B. TLymphozyten oder Monozyten, sind apoptotische Prozesse deutlich nachweisbar (Fesq, Bacher et al. 1994). Besonders schwere IAV-Infektionen werden meist im Kontext einer virusbedingten Lymphopenie beschrieben (Suarez and Schultz-Cherry 2000; Tumpey, Lu et al. 2000; Zitzow, Rowe et al. 2002). Für die Depletion von T-, B- und dendritischen Zellen werden in verschiedenen Studien vor allem extrinsische Faktoren wie Interferone oder die Liganden der TNF- (tumor necrosis factor) Familie verantwortlich gemacht (Toth, Szegezdi et al. 1999; Oh and Eichelberger 2000; Sedger, Hou et al. 2002). Die Depletion von Immunzellen verläuft zudem häufig synergistisch mit einer bakteriellen Koinfektion, weshalb schwere Krankheitsverläufe in einer durch bakterielle Superinfektion induzierten Pneumonie resultieren (Sweet and Smith 1980; Colamussi, White et al. 1999; Engelich, White et al. 11 Einleitung 2002). Die IAV-induzierte Apoptose verläuft überwiegend nach extrinsischen Mechanismen in einer autokrinen oder parakrinen Stimulation, wobei die Interferone-α/β und -γ sowie der TNF und TGF-β (transforming growth factor) als relevante pro-apoptotische Faktoren identifiziert wurden (Lowy 2003). Extrinsic pathway Intrinsic pathway 2.4 Schematische Darstellung der extrinsischen und intrinsischen apoptotischen Signalkasksade. Der extrinsische Pfad wird durch eine spezifische Ligand-Rezeptor-Bindung (TNF-Rezeptor, Fas/CD95) induziert, was zur Ausbildung eines DISC-Komplexes (death inducing signalling complex) führt. Durch die membranständige DISC-Formation werden mehrere Caspase 8 Moleküle rekrutiert, aktiviert und in das Zytosol freigesetzt. Die Caspase 8 ist je nach Zelltyp (Typ I+II) in der Lage, entweder direkt die zentrale Effektorcaspase-3 zu aktivieren oder durch die proteolytische Spaltung des pro-apoptotischen Bid-Proteins die mitochondriale Apoptose zu induzieren. Der intrinsische Pfad kann durch zelluläre Stresssignale oder nach einer Infektion durch pathogene Faktoren gezielt aktiviert werden, wie es beispielsweise für die akzessorischen Virusproteine Vpr (HIV), p13 (HTLV) oder PB1-F2 (IAV) bekannt ist. Im weiteren Verlauf erfolgt die Freisetzung von Cytochrom-c, dem AIF (apoptosis inducing factor) und SMAC (second mitochondria-derived activator of caspase) aus dem mitochondrialen Membranzwischenraum. Cytochrom-c bildet mit Apaf-1 (apoptotic protease activating factor) einen Komplex, der zunächst die Procaspase 9 und daraus folgend die Effektorcaspase-3 aktiviert. (Abbildung aus V.Jesenberger und S.Jensch, nature reviews, 2002). 12 Einleitung Weiterhin gibt es Befunde, die schwere, virusbedingte Gewebsschäden in der Lunge mit der Generierung von ROS-Radikalen (reactive oxigen species) in Verbindung bringen (Oda, Akaike et al. 1989). Gegenstand neuerer Untersuchungen ist die Rolle der Transaktivatoren NF-κB (nuclear factor kappa B) und AP-1 (activator protein 1), die zumindest indirekt durch die Modulation der Zytokin- und Interferonantwort sowie Aktivierung von Stress-Kinasekaskaden die apoptotischen Prozesse nach einer IAV-Infektion gleichsam regulieren (Pahl and Baeuerle 1995; Abraham, Stojdl et al. 1999; Balachandran, Roberts et al. 2000; Lin, Zimmer et al. 2001; Ludwig, Ehrhardt et al. 2001). Von zentraler Bedeutung ist das Fas-Rezeptor-System (Takizawa 93, Fujimoto 98), welches auch mit der Aktivierung der RNA-abhängigen Proteinkinase R (PKR) nach einer IAVInfektion in Zusammenhang gebracht wurde (Takizawa, Ohashi et al. 1996), wodurch der Zelltod letztlich über den FADD/Caspase8-Pfad (Fas-associated death domain protein) vermittelt wird (Balachandran, Roberts et al. 2000). Das Fas-FasL-System scheint weiterhin an der virusinduzierten humanen Lymphopenie beteiligt zu sein, da die CD95 Expression in CD 8+, 4+ und 3+ T-Zellen sowie in mononuklearen Leukozyten nach einer Infektion deutlich gesteigert ist (Nichols, Niles et al. 2001). Von den Virusproteinen wurden das NS1-Protein und das M1-Protein im Kontext pro-apoptotischer und anti-apoptotischer Prozesse beschrieben (Schultz-Cherry, Dybdahl-Sissoko et al. 2001; Zhirnov, Konakova et al. 2002; Zhirnov, Ksenofontov et al. 2002). Weiterhin ist bekannt, dass auch die virale NA proapoptotisch wirkt, da sie die latente Form des exogenen Apoptoseinduktors TGF-β aktiviert (Schultz-Cherry and Hinshaw 1996). Die Regulierung apoptotischer Prozesse nach einer IAV-Infektion wird durch die zellulären Caspasen vermittelt, wobei die zentrale Stellung der Effektorcaspase-3 bereits beschrieben wurde (Zhirnov, Konakova et al. 1999; Lin, Holland et al. 2002; Wurzer, Planz et al. 2003). Die Caspase-3 wird in einem Zeitraum von 12 h bis 36 h nach der IAV-Infektion aktiviert, wobei ihre Funktion für die Virusreplikation noch umstritten ist (Fesq, Bacher et al. 1994; Ludwig, Pleschka et al. 1999). Grundsätzlich wird die Apoptose als zellulärer Abwehrmechanismus gegen eine Vielzahl von Pathogenen betrachtet. Es konnte jedoch gezeigt werden, dass die Überexpression des anti-apoptotischen Proteins Bcl-2 in einer reduzierten Virusproduktion und HA-Fehlglykosylierung resultiert (Hinshaw, Olsen et al. 1994; Olsen, Kehren et al. 1996). Die Virusvermehrung ist in der Gegenwart von Caspase-3Inhibitoren ebenfalls stark eingeschränkt, was auch in Zellen gezeigt werden konnte, die shRNA gegen die Caspase-3 exprimierten (Wurzer, Planz et al. 2003). Dieser Effekt wird mit 13 Einleitung einer Retention des viralen RNP-Komplexes im Nukleus in Verbindung gebracht, die letztlich die Ausbildung von Viruspartikeln verhindert (Wurzer, Planz et al. 2003). Die Tatsache, dass das überexprimierte, virale NS1-Protein pro-apoptotisch wirkt, wurde als zusätzlicher Beleg dafür betrachtet, das die virusinduzierte Apoptose im Kontext einer produktiven Replikation steht (Schultz-Cherry, Dybdahl-Sissoko et al. 2001). Im Gegensatz hierzu konnte gezeigt werden, dass ein NS1-defizientes Virus in einer verstärkten Apoptoseinduktion resultiert und NS1 demnach anti-apoptotische Funktion besitzt (Zhirnov, Konakova et al. 2002), wofür auch die IFN-α/β-antagonistische Funktion des Proteins sprechen würde (Balachandran, Roberts et al. 2000). Weiterhin ist bekannt, dass das virale NP ein Substrat des Caspase-vermittelten proteolytischen Abbaus ist, was als ein zusätzliches Argument der antiviralen Funktion zellulärer Apoptose gilt (Zhirnov, Konakova et al. 1999). Ob die virusinduzierte Apoptose letztlich replikationsfördernde Elemente besitzt oder ein reiner zellulärer Abwehrmechanismus ist, bleibt Gegenstand weiterer Untersuchungen (Ludwig, Pleschka et al. 2006). 2.5 Die influenzainduzierte Signaltransduktion und die Rolle der PKC-Aktivierung Virale Infektionen resultieren in der unmittelbaren Aktivierung einer Vielzahl zellulärer Signale und Faktoren (Ludwig, Pleschka et al. 2006). In Zellkultur konnte gezeigt werden, dass nach einer IAV-Infektion alle bekannten Mitglieder der sogenannten MAPK-Familie (Mitogen-activated protein kinase) durch Phosphorylierungskaskaden aktiviert werden (Kujime, Hashimoto et al. 2000; Ludwig, Ehrhardt et al. 2001; Pleschka, Wolff et al. 2001). Zu ihnen zählen als Kinase-Prototypen ERK (extracellular signal regulated kinase), JNK (Jun-N-terminal kinase, BMK-1/ERK5 (Big MAP kinase) und die p38-MAPK (Pearson, Robinson et al. 2001). Durch die MAPK-Kaskade werden zelluläre Prozesse der Differenzierung und Proliferation wie auch die Aktivierung der Immunantwort reguliert (Dong, Davis et al. 2002). Beispielsweise resultiert die p38-MAPK-Aktivierung in der Expression von IL-8 (Interleukin-8) und des Chemokins RANTES (Regulated on Activation, Normal T Expressesd and Secreted), welches für das gezielte Rekrutieren von TLymphozyten und Makrophagen sowie von Eosinophilen und Neutrophilen an den Entzündungsherd von Bedeutung ist (Kujime, Hashimoto et al. 2000). Die von doppelsträngiger RNA (dsRNA) abhängige Aktivierung der Kinase-JNK hat einen deutlich antiviralen Effekt, da sie Prozesse in Gang setzt, welche die Expression des Zytokins IFNβ (Interferon β) induziert (Ludwig, Ehrhardt et al. 2001; Samuel 2001). Im Gegensatz hierzu scheint die Aktivierung der Raf/MEK/ERK-Kaskade für die Virus-Replikation von 14 Einleitung Vorteil zu sein (Pleschka, Wolff et al. 2001). Die Inhibition der Kinase-MEK oder Expression dominant-negativer ERK- oder Raf-Mutanten führten zur reduzierten Virusfreisetzung nach der Infektion durch das Influenza-A und -B-Virus (Ludwig, Wolff et al. 2004). Mechanistisch resultierte die ERK-Inhibition in der Retention der viralen RNP-Komplexe im Zellkern, was sich unmittelbar auf die Replikation auswirkt. Da die Inhibition der Kinase MEK virusspezifisch und effektiv gegen beide Virusgattungen wirkt, werden MEK-Inhibitoren als antivirale Substanzen für eine eventuelle klinische Anwendung zur Zeit untersucht (Planz, Pleschka et al. 2001; Ludwig, Pleschka et al. 2006). Ein weiterer wichtiger Faktor, der nach einer IAV-Infektion durch die Akkumulation viraler RNA und anschließender IKKβ-Stimulation aktiviert wird, ist der IκB/NFκB Kinasekomplex (Julkunen, Melen et al. 2000; Hiscott, Kwon et al. 2001). Durch Phosphorylierung des NFκBInhibitors IκB (inhibitor of NFκB) erfolgt dessen proteasomaler Abbau und die Translokation des NFκB-Dimers in den Zellkern (Ghosh, May et al. 1998; Karin and Delhase 2000). Die Transkriptionsfaktoren, welche zur NF-κB-Familie zählen, regulieren über 150 verschiedene Gene, welche hauptsächlich immunologische und inflammatorische Prozesse steuern, unter anderem die Expression von Zytokinen, Chemokinen sowie von pro- und anti-apoptotischen Proteinen (Pahl 1999). Gleich der Kinase JNK reguliert auch die NFκB-Aktivierung die Expression der bedeutenden antiviralen Faktoren IFNβ und TNFα (Maniatis, Falvo et al. 1998; Chu, Ostertag et al. 1999; Taniguchi and Takaoka 2002). Eine weitere Kinase, die häufig im Kontext viraler Infektionen beschrieben wurde und eine Vielzahl von Effektor-Signalkaskaden reguliert, ist die Proteinkinase C (PKC) (Constantinescu, Cernescu et al. 1991; Toker 1998; Warrilow, Gardner et al. 2006). Die PKCFamilie besteht aus 13 bekannten Isoformen (Tab. 2), welche in 3 Klassen unterteilt werden können, basierend auf der Abhängigkeit von Ca2+ und Phorbolesteraktiverung (Abb. 2.5.1) (Li and Gobe 2006). PKC Subfamilie Isoforme cPKC α, βI, βII, γ nPKC Δ, ε, η, θ, ζ aPKC ξ, ι/λ, ν, μ Tab.2 Die Protein-Kinase-C-(PKC)-Subfamilien und ihre Isoformen. Die PKC Familie wird in die konventionellen (cPKC), neuartigen (nPKC) und atypischen (aPKC) unterteilt. Zum aktuellen Zeitpunkt sind 13 Isoforme bekannt. 15 Einleitung Abb. 2.5.1 Schematischer Aufbau der PKC-Subfamilien. Die verschiedenen Subtypen lassen sich in vier konservierte (C 1-4) und fünf isoenzym-spezifische, variable (V 1-5) Regionen unterteilen. Die Mitglieder der konventionellen PKC Isoformen besitzen neben der C-terminalen katalytischen Domäne auch eine Ca2+-, Phosphatidylserin (PS)- und Diacylglycerin (DAG)-Bindestelle, welche alle zur vollständigen Aktivierung benötigt werden. Die neuartigen und atypischen PKC Isoformen sind Ca2+-unabhängig. Die Bedeutung der PKC hinsichtlich der Regulation des Viruseintritts in die Zellen konnte durch die PKC-Inhibitoren Staurosporin und H7 für verschiedene umhüllte Viren gezeigt werden (Vesicular stomatitis-virus, herpes simplex-I, vaccinia virus, poliomyelitis virus) (Constantinescu, Cernescu et al. 1991). Nach einer IAV-Infektion oder HA-Inkubation von Zellen konnte eine sofortige Aktivierung der konventionellen PKC Isoformen detektiert werden (Arora and Gasse 1998; Kunzelmann, Beesley et al. 2000; Root, Wills et al. 2000). Der PKC spezifische Inhibitor Bisindolylmaleimid (BIM), sowie eine Reihe hochselektiver Inhibitoren (CalphostinC, Gö6976) waren in der Lage, den frühen IAV-Eintrittsprozess in die Zelle dosisabhängig und reversibel zu inhibieren (Abb. 2.5.2) (Root, Wills et al. 2000). Durch die Expression einer phosphorylierungs-defizienten Mutante und den Einsatz selektiver PKC-Inhibitoren, konnte eine Funktion der PKCβII-Isoform im Kontext der Regulation der späten Endosomen und blockierter RNP-Freisetzung identifiziert werden (Sieczkarski, Brown et al. 2003). Die PKC-Aktivierung betrifft jedoch auch Ereignisse des späten Replikationszyklusses durch die indirekte Regulation von Effektormolekülen in der Signaltransduktion. Beispielsweise wird die Phosphorylierung der Raf-Kinase ebenfalls durch verschiedene PKC-Isoforme reguliert (Kolch, Heidecker et al. 1993; Cai, Smola et al. 1997), was letztlich in der Aktivierung der mitogenen Raf/MEK/ERK-Kaskade resultiert (siehe oben). Die Aktivierung der PKCα durch HA-Akkumulation an den lipid rafts in späten Stadien des Replikationszyklusses und die daraus resultierende Raf-Phosphorylierung konnte sogar direkt bestätigt werden (Abb. 2.5.2), (Marjuki, Alam et al. 2006). Auch wenn die genauen Mechanismen der PKC-Aktivierung durch das Influenza-A-Virus und deren Interaktion mit der zellulären Signaltransduktion noch nicht geklärt sind, zeichnet sich 16 Einleitung dennoch die zentrale Rolle der konventionellen-α/β-Isoformen ab, welche ubiquitär in allen bisher untersuchten Zellen vorhanden sind (Li and Gobe 2006). Abb. 2.5.2 Die Rolle der PKC-Aktivierung im Replikationszyklus von IAV. Nach der Infektion bzw. HA-Inkubation von Zellen erfolgt die Aktivierung der konventionellen PKCßII-Kinase, die vom Zytosol zur Zellmembran transloziert und über den N-Terminus der regulatorischen Domäne (R) im Zytoplasma verankert ist. Die katalytische Domäne (C) wird durch diesen Vorgang durch eine Konformationsänderung freigesetzt und aktiviert. Die spezifische und selektive Inhibition der PKC oder die Expression einer funktionell depletierten PKC-Mutante (dnPKCβII) resultiert in der Retention der viralen RNPs im späten Endosom. Im Gegensatz hierzu wird erst spät im Replikationszyklus die Raf/MEK/ERK-Kaskade durch die Einlagerung von HA-Proteinen in lipid-rafts während der VirusAssemblierung aktiviert. Die gezielte Inhibition der PKCα resultierte in einem analogen Aktivitätsverlust der ERK-Kinase und der RNP-Retention im Nukleus. 2.6 PB1-F2, das 11. Influenzaprotein Im Jahr 2001 wurde ein elftes IAV-Genprodukt mit der Bezeichnung PB1-F2 beschrieben (Chen, Calvo et al. 2001). Entdeckt wurde das Protein bei einem Screening nach MHC-I Epitopen, die sich von viralen Polypeptiden ableiten lassen, die außerhalb des StandardLeserahmens der Influenza-Virusproteine exprimiert werden. PB1-F2 ist das einzige IAVProtein, welches in einem zweiten, alternativen +1-Leserahmen (F2, frame 2) kodiert wird, der innerhalb des pb1-Gens der viralen RNA-Polymerase (PB1) liegt (Abb. 2.6.1). Dies wird 17 Einleitung durch das sogenannte „ribosomale Scanning“ ermöglicht, einem Vorgang, bei dem die 40SUntereinheit des Ribosoms nach weiteren AUG Startcodons innerhalb eines Leserahmens „scannt“, um die Translation zu initiieren (Jackson 2005). Voraussetzung hierfür ist eine ideale Initiationssequenz, welche auch als „Kozaksequenz“ (Kozak 1991) bezeichnet wird und am Startcodon von PB1-F2 vorhanden ist. Abb. 2.6.1 DNA und Aminosäuresequenz von PB1-F2 im Leserahmen von PB1. Das PB1-F2 Startcodon (rot) befindet sich downstream vom bekannten ATG Initiations-Triplett (gelb, unterstrichen) und zwei weiteren potentiellen ATG-Abfolgen (gelb) (Abbildung verändert nach Chen et al. 2001). Das vom IAV-Laborstamm A/PuertoRico/8/34(H1N1) (IAVPR8) exprimierte Protein, welches in anfänglichen Studien untersucht wurde, hat ein Molekulargewicht von 11 kDa und eine Länge von 87 A.s. (Chen, Calvo et al. 2001). Die neuesten Sequenzanalysen zeigen, dass PB1-F2 in den meisten humanen und Vogelgrippe-Isolaten als funktionelles Protein mit einer Länge von 78 bis 90 A.s. vorliegt. In Influenza-B-Virusisolaten ist PB1-F2 nicht präsent (Chen, Calvo et al. 2001; Zell, Krumbholz et al. 2007). Interessanterweise exprimiert ein Großteil der seit 1950 zirkulierenden humanen H1N1-Isolate ein C-terminal verkürztes PB1F2 mit einer Länge von nur 57 A.s. (Zell, Krumbholz et al. 2007). Strukturanalysen vorangegangener Arbeiten haben gezeigt, dass PB1-F2 unter hydrophoben Bedingungen zwei kleinere α-Helices im N-Terminus und eine große α-Helix von Position Ile-53 bis Lys-85 im C-Terminus ausbildet (Abb. 2.6.2) (Bruns, Studtrucker et al. 2007). Der strukturierte CTerminus umfasst alle bis jetzt beschriebenen funktionellen Regionen des Proteins. Zu ihnen zählen die Oligomerisierungsdomänen (OD), welche für die intrinsische Fähigkeit von PB1F2 verantwortlich sind, Dimere und Multimere auszubilden, und die mitochondriale Zielseqeunz (MTS) (Gibbs, Malide et al. 2003; Bruns, Studtrucker et al. 2007). Es wird spekuliert, dass die Oligomerisierung von PB1-F2 der Funktion dient, Poren in biologischen Membranen auszubilden, was für eine mögliche Destabilisierung der mitochondrialen 18 Einleitung Membran und anschließender Depolarisierung des Membranpotentials von Bedeutung sein könnte (Chanturiya, Basanez et al. 2004; Zamarin, Garcia-Sastre et al. 2005). Weiterhin Abb. 2.6.2 Sekundärstruktur des PB1-F2-Proteins vom IAV-Stamm A/Puerto Rico/8/34 (H1N1) mit allen bisher bekannten funktionellen Domänen und C-terminaler α-Helix. konnte gezeigt werden, dass virales PB1-F2 nach radioaktiver 35S Markierung von infizierten MDBK-Zellen in drei kurz aufeinanderfolgenden Banden im SDS-Gel migriert, was auf einer möglichen posttranslationalen Modifikation des Proteins beruhen könnte (Chen and Holmes 2008). Erste in-silico-Sequenzanalysen gaben Hinweise darauf, dass PB1-F2 mehrere potentielle Phosphorylierungsstellen besitzt, was im Rahmen dieser Arbeit experimentell bestätigt werden konnte (Henklein, Bruns et al. 2005). Die exakte biologische Funktion von PB1-F2 und seine Bedeutung im Kontext der zellulären IAV-Replikation sind bis heute ungeklärt. Ursprünglich wurde PB1-F2 als pro-apoptotisch und als ein Verstärker der IAV-induzierten Apoptose in infizierten Monozyten beschrieben (Chen, Calvo et al. 2001). Das Protein ist sowohl im Zytoplasma als auch in den Mitochondrien von transfizierten und infizierten Zellen lokalisiert und ist bei Letzteren partiell auch im Nukleus vorzufinden (Chen, Calvo et al. 2001). Die mitochondriale Lokalisation von PB1-F2 und der Befund, dass die Präsenz von nanomolaren Mengen an synthetischem sPB1-F2 im Zellkulturmedium zur Cytochrom-c Freisetzung in HeLa-Zellen führt, gaben Hinweise darauf, dass PB1-F2 das erste IAV-Protein ist, das den intrinsischen Apoptosepfad induziert (Chen, Calvo et al. 2001; Lowy 2003). Andererseits wurde berichtet, dass Plasmid-exprimiertes PB1-F2 nicht ausreichend ist, um in Epithelzellen Apoptose auszulösen. In der Gegenwart von apoptotischen Stimuli wie UV-Strahlung oder Cisplatin konnte jedoch eine verstärkte Apoptoseinduktion in PB1-F2 transfizierten 293T-Zellen im Vergleich zu nicht transfizierten Zellen beobachtet werden (Zamarin, Garcia-Sastre et al. 2005). In Koimmunopräzipitationsstudien wurden die beiden Untereinheiten des mitochondrialen PTPC (Permeabiltiy transition Pore complex) als zelluläre Bindungspartner von PB1-F2 identifiziert (Zamarin, Garcia-Sastre et al. 2005). Ob PB1-F2 durch diese Interaktion pro-apoptotische Prozesse vermittelt oder durch seine multimerisieren und Membranporen zu bilden, ist bis heute nicht geklärt. 19 Fähigkeit zu Einleitung Für die virale Replikation scheint PB1-F2 entbehrlich zu sein, was sowohl in Zellkultur als auch nach der Infektion von Mäusen gezeigt werden konnte (Zamarin, Ortigoza et al. 2006). Ein attenuiertes Virus eines mauspathogenen WSN-Isolates, das nicht mehr in der Lage ist, PB1-F2 zu exprimieren, zeigte in den Lungen der Tiere während den ersten 3 Tagen nach der Infektion vergleichbare Titer wie das Wildtyp-Virus. PB1-F2 scheint vielmehr als akzessorisches IAV-Protein von Bedeutung zu sein, ähnlich dem Influenza-NS1-(non structural 1)-Protein, von dem bekannt ist, dass es die virusinduzierte Apoptose reguliert (Zhirnov, Konakova et al. 2002; Lowy 2003) und die antiviralen Mechanismen der Wirtszelle durch die Inhibition der Typ-1-Interferonantwort reprimiert (Zhirnov, Konakova et al. 2002; Lowy 2003). Des Weiteren hat PB1-F2 funktionelle Ähnlichkeiten mit anderen proapoptotischen Hilfsproteinen, wie z.B. dem p13-Protein von HTLV (D'Agostino, Ranzato et al. 2002; Silic-Benussi, Cavallari et al. 2004) oder dem Vpr-Protein von HIV-1 (Muthumani, Hwang et al. 2002; Sherman and Greene 2002), welche ebenso in den Mitochondrien und dem Nukleus von infizierten Zellen lokalisiert sind. Neuere Daten lassen darauf schließen, dass PB1-F2 als Pathogenitätsfaktor vor allem im Kontext hochpathogener Isolate von Bedeutung sein könnte (Zamarin, Conenello, Auley). So wurden in den Lungen von Mäusen, die mit einem PB1-F2-exprimierenden Virus vom WSN-Isolat infiziert waren, nach sechs Tagen deutlich mehr Viruspartikel detektiert als in den Lungen der Tiere, die mit einem rekombinanten, PB1-F2 defizienten Virus desselben Isolates infiziert wurden (Zamarin, Ortigoza et al. 2006). Dieser Befund bekräftigte die Hypothese, dass PB1-F2 immunmodulatorische Funktion besitzt, da die Virusneutralisierung durch das Immunsystem des Wirtes in einem noch nicht bekannten Mechanismus in Abhängigkeit von PB1-F2 verzögert wird. Interessanterweise war ein Aminosäureaustausch innerhalb der PB1-F2Sequenz von Asn-66 zu Ser-66 ausreichend, um ein Virus von moderater Pathogenität (H5N1, HK/156/97) in ein hochpathogenes zu konvertieren (Conenello, Zamarin et al. 2007). Ebenso zeigte ein rekombinantes IAV-Isolat der Spanischen Grippe, das für PB1-F2 in Position 66 mutiert war, eine deutlich geringere Lethalität in infizierten Mäusen als das Wildtyp-Virus. Neuere Studien zeigten, dass PB1-F2 in der Lage ist, die Pathogenität der virusinduzierten und sekundären bakteriellen Pneumonie zu verstärken (McAuley, Hornung et al. 2007). Um die PB1-F2-spezifischen Effekte zu untersuchen, wurde ein mausadaptiertes PR8-Isolat mit dem PB1-F2-Knock-out-Virus desselben Isolates verglichen. Die bakterielle Koinfektion mit Streptococcus pneumoniae erfolgte sieben Tage nach der Virusinfektion. Dabei zeigte sich, dass die Expression von PB1-F2 im Vergleich zum PB1-F2-defizienten Virus mit einer erhöhten Zahl an Neutrophilen, Makrophagen und T-Zellen in der Lungenlavage der Tiere 20 Einleitung und mit einer gesteigerten Entzündung des alveolaren Parenchyms korreliert. Vergleichbare Effekte wurden erzielt, wenn die Tiere mit einem synthetischen Peptid behandelt wurden, das den C-Terminus von IAVPR8 einschließlich der MTS umfasst. Die anschließende bakterielle Infektion führte innerhalb von acht Tagen zum Tod aller Tiere, die mit dem C-terminalen Peptid vorbehandelt wurden, wohingegen ein N-terminales Kontrollpeptid keine Mortalität in den Tieren induzierte. Noch dramatischere Effekte zeigten sich nach der Infektion mit einem rekombinanten PR8-Virus, dessen PB1-F2-Protein durch gezielte Mutationen an die Sequenz des Proteins aus einem Isolat der Spanischen Grippe von 1918 angepasst wurde (McAuley, Hornung et al. 2007). Im Gegensatz zum PR8- und WSN-Wildtyp-Virus zeigte sich eine gesteigerte Virulenz, die durch größere Plaque-Morphologie und schnellere Virusreplikation innerhalb der ersten Tage nach der Infektion in Zellkultur angezeigt wurde. Zusätzlich wurden die inflammatorischen Effekte in Mäusen im Kontext einer bakteriellen Koinfektion in Gegenwart des PB1-F2-Proteins der Spanischen Grippe im Vergleich zum Wildtyp-PR8Isolat dramatisch gesteigert. Diese Ergebnisse sind von großer Bedeutung, da die Hauptursache für die hohen Sterblichkeitsraten, welche von einigen humanpathogenen Influenzavarianten hervorgerufen werden, in einer sekundären, bakteriellen Superinfektion begründet ist, die zu lebensgefährlichen Pneumonien führen kann (Beveridge 1991; McCullers 2006). Erst vor kurzem wurde das virale PB1-Protein als Interaktionspartner von PB1-F2 beschrieben (Mazur, Anhlan et al. 2008). In Koimmunopräzipitationsstudien konnte gezeigt werden, dass PB1-F2 das PB1-Protein, aber nicht PB2, NP oder M1 präzipitiert, was weitestgehend die Möglichkeit ausschließt, dass PB1-F2 ein Teil des RNP-Komplexes ist. Die Interaktion könnte jedoch für eine zeitlich regulierte Retention des PB1-Proteins im Nukleus verantwortlich sein, da in einem PB1-F2-defizienten Virus das PB1-Protein für 7 h nach der Infektion im Zytoplasma lokalisiert ist, wohingegen es im Wildtyp-Virus zu diesem Zeitpunkt noch überwiegend im Nukleus zu finden ist. Die Interaktion von PB1-F2 und PB1 könnte auch für die unterschiedliche Plaque-Morphologie verantwortlich sein, die mehrfach in Abhängigkeit von PB1-F2 detektiert wurde (McAuley, Hornung et al. 2007; Mazur, Anhlan et al. 2008). Das zuvor erwähnte rekombinante PR8-Isolat, welches eine PB1-F2-Variante der Spanischen Grippe exprimiert, bildete in Zellkultur größere Plaques aus als der Wildtpy (McAuley, Hornung et al. 2007). Der gleiche Effekt wurde nach der Infektion von IAVPR8Virus im Vergleich zur PB1-F2-defizienten Mutante beobachtet. In Abwesenheit von PB1-F2 war die Plaque-Größe deutlich reduziert (Mazur, Anhlan et al. 2008). Die Mechanismen der PB1-F2-vermittelten Phänomene sind bis heute nicht geklärt. Vor allem im Kontext 21 Einleitung hochpathogener Isolate zeichnet sich die Bedeutung dieses scheinbar multifunktionellen Proteins zusehends ab, weshalb PB1-F2 inzwischen zu Recht als kleines Protein mit großer Wirkung bezeichnet wird (Conenello and Palese 2007). 22 Zielsetzung 3. Zielsetzung Im Rahmen dieser Arbeit sollten zunächst die molekularen Mechanismen der proapoptotischen Funktion von PB1-F2 in Zellkultur untersucht werden. Vor allem sollte geklärt werden, ob und wie extrazelluläres PB1-F2 zytotoxische Effekte vermittelt und somit ähnlich dem Vpr-Protein von HIV-1 transduzierende Eigenschaften besitzt. Für das neuartige PB1-F2-Protein waren bisher keinerlei posttranslationale Modifikationen bekannt. Da Virusproteine häufig multifunktionell und modifiziert sind, sollte durch in-vitround in-vivo-Experimente untersucht werden, ob PB1-F2 ein Phosphoprotein darstellt und wenn ja, welche Funktionen durch diese Modifizierung reguliert werden. Abschließend wurde die inhärente Eigenschaft von PB1-F2 untersucht, Dimere und Multimere auszubilden. Dabei sollte geklärt werden, ob die Oligomerisierung von PB1-F2 durch Disulfidbrücken oder spezifische Multimerisierungsdomänen vermittelt wird, und in welcher Region des Proteins enstprechende Sequenzabschnitte lokalisiert sind. 23 Material und Methoden 4. Material und Methoden 4.1 Material 4.1.1 Verbrauchsmaterial 1,5 ml Reaktionsgefäße 15 ml Reaktionsgefäße 50 ml Reaktiongefäße Zellkultur-Platten BioMax-Filme MR Zellkultur-Cryo-Gefäße Sarstedt, Nümbrecht BD Falcon, Heidelberg BD Falcon, Heidelberg BD Falcon, Heidelberg Kodak, Stuttgart Nunc, Wiesbaden Hybond-P Polyvinylidenfluorid (PVDF)-Membran Amersham Biosciences, Freiburg Mikropipettenspitzen Reaktionsgefäße für die PCR Serologische Pipetten Whatman-Papier Zellkulturflaschen Zellkulturschalen Greiner, Frickenhausen Biozym, Oldendorf Corning, Schiphol-Rijk, Niederl. Whatman, USA Nunc, Wiesbaden BD Falcon, Heidelberg 4.1.2 Chemikalien und Reagenzien Produkt 2-Mercaptoethanol Acrylamid (30%), Bisacrylamid (1%) Adenosin-5’Triphosphat (ATP) Agar (gereinigt) Albumin (Protease frei) Ammoniumperoxidsulfat (APS) Ampicillin Annexin-V BioRad Protein Assay-Stammlösung Bisindolylmaleimid Bis(sulfosuccinimidyl)suberat (BS3) Bovines Albumin 35% Bromphenolblau Coomassie-Brilliant Blue R-250 Calciumchlorid Cisplatin D-MEM (4500 mg/l Glucose, GlutaMAXI) DEAE Dextran DMSO (Dimethylsulfoxid) Dithiotreitol (DTT) Disuccinimidylsuberat (DSS) EDTA (Na-Ethylendiamintetraacetat) Essigsäure Ethanol, technisch (96%) Ethidiumbromid Ethylenglykol Disuccinat Etoposid Fötales Kälberserum (FCS) Hersteller Roth (Karlsruhe) Roth (Karlsruhe) Sigma (St.Louis) Oxoid (Wesel) Roth (Karlsruhe) Roth (Karlsruhe) Sigma (St. Louis, USA) Invitrogen (Hamburg) BioRad (München) Calbiochem (Schwalbach) Pierce (Rockford, USA) MP Biomedicals Fluka (Buchs, Schweiz) Fluka (Buchs, Schweiz) Fluka (Buchs, Schweiz) Sigma (St. Louis, USA) Gibco/PAA (Paisley) Amersham (Little Chalfont) Sigma (St. Louis) Roth (Karlsruhe) Pierce (Rockford, USA) Roth (Karlsruhe) Roth (Karlsruhe) Roth (Karlsruhe) Roth (Karlsruhe) Pierce (Rockford, USA) Calbiochem (Schwalbach) PAA (Pasching) 24 Material und Methoden D(+)-Glucose Glutaraldehyd (GA) Glycerin Glycin Glycerol HEPES Isopropanol JC1 Kaliumchlorid Lipofectamin 2000 Magnesiumchlorid-Hexahydrat MEM (+GlutaMAX I) MEM 10x (-L-Glutamin, -NaHCO3) Methanol Milchpulver Natriumacetat Natiumazid Natriumchlorid Natriumdodecylsulfat (SDS) Natriumhydroxid Natriumhydrogenphosphat Natriumorthovanadat Nonidet P40 OptiMEM I Orthophosphat 32P PBS 1x Penicillin/Streptamycin Phorbol 12-myristat 13-acetat (PMA) PMSF Propidiumiodid Protein Ladder (Page Ruler) Protein G-Sepharose RPMI 1640 Staurosporin Salzsäure SDS (Sodium Dodecylsulfat) Tris Triton X-100 Trypanblau Tween 20 Wasserstoffperoxid 30% Roth (Karlsruhe) Pierce (Rockford, USA) Roth (Karlsruhe) Roth (Karlsruhe) Sigma (St. Louis) Roth (Karlsruhe) Roth (Karlsruhe) Sigma (St. Louis, USA) Roth (Karlsruhe) Gibco (Paisley) Roth (Karlsruhe) Gibco (Paisley) Gibco (Paisley) Fluka (Buchs, Schweiz) Saliter (Obergünzburg) Roth (Karlsruhe) Roth Karlsruhe) Roth (Karlsruhe) Roth (Karlsruhe) Roth (Karlsruhe) Roth (Karlsruhe) Sigma (St. Louis, USA) Sigma (St. Louis, USA) Gibco (Paisley) Amersham (Uppsala, Schweden) Invitrogen (Karlsruhe) Invitrogen (Karlsruhe) Sigma (St. Louis, USA) Sigma (St. Louis, USA) Invitrogen (Hamburg) Fermentas (Litauen) Amersham (Uppsala, Schweden) Gibco (Paisley) Calbiochem (Darmstadt) Roth (Karlsruhe) Sigma (St. Louis, USA) Roth (Karlsruhe) Sigma (St. Louis, USA) Gibco (Paisley) Sigma (St. Louis) Merck (Darmstadt) 4.1.3 Standard Puffer und Lösungen je 2,5 mM (Fa. Eppendorf, Hamburg) Desoxyribonukleotide (dATP, dCTP, dGTP, dTTP) 50 mg Luminol (Fa. Sigma, Deisenhofen) in 200 ml 0,1 M ECL-Lösung A Tris/HCl, pH 8,6 11 mg p-Hydroxycumarinsäure (Fa. Sigma, Deisenhofen) in ECL-Lösung B 10 ml DMSO 25 Material und Methoden 0,1 % (v/v) Tween 20 in PBS 1M Tris-HCl, pH 6.8 1,5 M Tris-HCl, pH 8.8 Tris, pH 6.8 x) 25 mM 192 mM Glycin 0,1% (w/v) SDS 100 mM Tris pH 6.8 SDS-Probenpuffer (1 x) 2 % (w/v) SDS 5 % (v/v) Glyzerol 10 % (v/v) ß-Mercaptoethanol 0,02 % (w/v) Bromphenolblau 10 mM Tris-HCl, pH 8.0 TE-Puffer 1 mM EDTA 40 mM Tris-HCl TAE-Puffer (1 x) 20 mM Natriumacetat Tris 25 mM Glycin 192 mM Transferpuffer (1 x) 10% (v/v) Methanol (nach Towbin) Coomassie Brilliant Blau R 250 0.5% (w/v) Coomassie-Färbelösung Isopropanol 25% (v/v) 10% (v/v) Essigsäure 25% (v/v) Isopropanol Coomassie10% (v/v) Essigsäure Entfärbelösung PBS-Tween Sammelgelpuffer Trenngelpuffer SDS-Laufpuffer (1 (nach Laemmli) 4.1.4 Synthetische Peptide Synthetisches PB1-F2 (sPB1-F2) wurde unter Verwendung der solid phase peptide synthesis (SPPS) und der anschließenden nativen chemischen Ligation (NCL) synthetisiert (Henklein et al. 2005; Röder et al. 2008). Bezeichnung sPB1-F2 (PR8) Isolat A/Puerto Rico/8/34(H1N1) Herkunft Henklein, Charite Berlin NH2-MGQEQDTPWI-LSTGHISTQK-RQDGQQTPKL-EHRNSTRLMG-HCQKTMNQVVMPKQIVYWKQ-WLSLRNPILV-FLKTRVLKRW-RLFSKHE-COOH sPB1-F2 (SFII) A/Brevig Mission/1/18 (H1N1) Henklein, Charite Berlin NH2-MGQEQDTPWI-LSTGHISTQK-REDGQQTPRL-EHHNSTRLMD-HCQKTMNQVVMPKQIVYWKQ-WLSLRSPTPV-SLKTRVLKRW-RLFSKHEWTS-COOH sPB1-F2 (BFII) Konsensussequenz (H5N1) Henklein, Charite Berlin NH2-MEQEQDTPWT-QSTEHINIQK-RGNGQRTQRL-EHPNSIRLMD-HCLRIMSRVGMHKQIVYWKQ-WLSLKNPTQG-SLKTRVLKRW-KLFSKQEWIN – COOH sPB1-F2 (20mer) Fragmente (Henklein et al. 2005) A/Puerto Rico/8/34(H1N1) 4.1.5 Antikörper AntiInfluenza A/PR8/34-PB1-F2, polyklonal Henklein, Charite Berlin Bezugsquelle Seramun, (Henklein, Bruns et al. 2005) 26 Material und Methoden Influenza-A PB1, monoklonal Influenza-A NP, polyclonal PARP, monoklonal GFP, monoklonal ß-Aktin, nonoklonal anti-mouse, IgG-HRP anti-rabbit, IgG-HRP Santa Cruz (Heidelberg) Serotec (Düsseldorf) BD Bioscience (San Jose, USA) Gene Tex Sigma Amersham (Little Chalfont) Amersham (Little Chalfont) 4.1.6 Plasmide und Oligonukleotide Plasmide Plasmide pBC12/CMV MCSI pBC12/CMV PB1-F2 pBC12/CMV PP1-F2-His pBC12/CMV PB1-F2-S35/N pBC12/CMV PB1-F2-T27/N pBC12/CMV PB1-F2-S84/N pBC12/CMV PB1-F2-T27,S35/N pHW2000 PB1 pcDNA3 Herkunft Stratagene (Heidelberg) Nicole Studtrucker Nicole Studtrucker David Mitzner David Mitzner David Mitzner David Mitzner Anhlan Darisuren (Münster) Invitrogen (Karlsruhe) Oligonukleotide Die aufgeführten Oligonukleotide wurden von der Fa. Biomers (Ulm) bezogen und für die Mutagenese-PCR der PB1-F2 Phosphorylierungsstellen verwendet. Name Sequenz P27(5’) P27(3’) P35(5’) P35(3’) P84(5’) P84(3’) 5’-AAGATGGACAACAAAACCCGAAACTGGAGCAC-3’ 5’-GTGCTCCAGTTTCGGGTTTTGTTGTCCATCTT-3’ 5’-CTGGAGCACCGCAACAACACCCGATTGATGGGC-3’ 5’-GCCCATCAATCGGGTGTTGTTGCGGTGCTCCAG-3’ 5’-GATGGAGGTTGTTCAACAAACACGAGGCGGG-3’ 5’-CCCGCCTCGTGTTTGTTGAACAACCTCCATC-3’ 4.1.7 Bakterien und Bakterienkulturreagenzien Bakterien Für Transformationen wurde der ultrakompetente Escherichia coli (E. coli) Stamm XL2-blue (Stratagene, Heidelberg) verwendet. Die Lagerung erfolgte bei -80°C. 27 Material und Methoden Bakterienkulturreagenzien 1 % (w/v) LB-Medium 0,8 % (w/v) 0,5 % (w/v) LB–Agarplatten Pepton NaCl Bacto-Hefe-Extrakt pH 7.2; autoklaviert Bactoagar in LB-Medium 1,5 % (w/v) Zur Selektion transformierter Bakterienklone wurde dem Kulturmedium, bzw. den LBAgarplatten Ampicillin in einer Endkonzentration von 100 μg/ml zugesetzt. 4.1.8 Eukaryotische Zellen und Medien Eukaryotische Zelllinien und primäre Zellen Humane Zervixkarzinomzelllinie (Scherer et al. 1953). HeLa SS6: HEK 293T: Humane embryonale Nierenzelllinie (HEK: „human embryonic kidney“). Diese Zellen wurden durch Einbringen von gescherter Adenovirus-DNA in embryonale Zellen hergestellt (Graham, Smiley et al. 1977). Die Zelllinie 293T ist ein Subklon, der zusätzlich das SV40 (simian virus 40) T-Antigen exprimiert. Jurkat T-Zell Leukämiezelllinie (Weiss, Wiskocil et al. 1984). MDCK Madin Darby Canine Kidney, Nierenkarzinom vom Cockerspaniel, entnommen 1958. MDBK Madin Darby Bovine Kidney, Nierenkarzinom vom Rind, entnommen 1957. Primäre Monozyten Aufgereinigte humane Spender-Monozyten (Reinheit 7095%, CD14+) wurden von der Dermatologie der Universitätsklinik Erlangen bezogen (Erdmann, Dorrie et al. 2007). Dendritische Zellen Dendritische Zellen wurden von der Dermatologie der Universitätsklinik Erlangen bezogen (Prof. Dr. Steinkasserer). Zellkulturmedien Die Zellkulturmedien DMEM (Dulbecco’s modified eagle medium), MEM (Minimum Essential Medium) bzw. RPMI (Roswell Park Memorial Institute), wurde von der Fa. Gibco/BRL, Karlsruhe bezogen und mit 10 % (v/v) hitzeinaktiviertem FKS (Fa. Gibco/BRL, 28 Material und Methoden Karlsruhe), 2 mM L-Glutamin, 170 mM Penicillin und 40 mM Streptomycin (Fa. Sigma, Deisenhofen) supplementiert. Für die Monozytenkultivierung wurde DMEM mit 10 % (v/v) humanem Serum, 1% Natriumpyruvat (SIGMA), 170 mM Penicillin und 40 mM Streptomycin verwendet. 4.1.9 Virus-Stocklösungen Stamm Herkunft Humanes IAV Virusisolat recA/Puerto-Rico/8/34(H1N1) (PR8) Anhlan Darisuren (Münster) Rekombinanten humanes Virusisolat A/Puerto-Rico/8/34 Anhlan Darisuren (Münster) (H1N1) (PR8) F2C (PB1-F2 ATG95→ACG) Rekombinanten humanes Virusisolat A/Puerto-Rico/8/34 Anhlan Darisuren (Münster) (H1N1) (PR8) F2C (PB1-F2 ATG95→ACG, TCA128→TGA) Wird auch als IAVPR8(2xΔF2) bezeichnet. Rekombinanten humanes Virusisolat A/Puerto-Rico/8/34 Anhlan Darisuren (Münster) (H1N1) (PR8) F2C (PB1-F2 Thr198→Ile, Ser222→Leu) 4.2 Methoden 4.2.1 Standardmethoden - PCR Produkte wurden mit dem QIAquickTM PCR Purification Kit von Quiagen (Hilden) aufgereinigt. - Agarosegelelektrophorese wurde nach Sambrook (Sambrook, 1989) durchgeführt. - Die präparative Plasmidisolierung wurde mit dem QIAprep Miniprep Kit oder dem Plasmid Maxi Kit der Firma Qiagen (Hilden) durchgeführt. - Seqeunzierungen von DNA wurden mit dem BigDye3.1TM Sequenzierer der Firma ABI (Weiterstadt) in dem Gerät Master Cycler Gradient der Firma Eppendorf (Hamburg) amplifiziert, aufgereinigt, und in dem Sequenzier-Automaten ABI PRISM 3100 der Firma Applied Biosystems (USA) analysiert. Die Auswertung der Sequenzen erfolgte durch das Programm VectorNTI 7.0. - Die Mutagenese PCR QuikChange® II wurde nach den Herstellerangaben (STRATAGENE, La Jolla, USA) durchgeführt. - Die Anzucht und Transformation von E.coli erfolgte nach den von Ausubel und Sambrook beschriebenen Protokollen (SAMBROOK 1989). - Die photometrische Bestimmung der DNA-Reinheit und -Konzentration wurde nach Standardprotokollen vorgenommen (SAMBROOK 1989). 29 Material und Methoden - Lipofektamintransfektion erfolgte mit dem Reagenz Lipofectamine2000 der Firma Invitrogen (Karlsruhe) nach den Herstellerangaben. - Proteinkonzentrationen wurden mit Hilfe des BCATM Protein Assay der Firma Pierce (USA) in dem ELISA-Reader Soft Max Pro (Molecular Devices, USA) quantitativ bestimmt. - Proteine wurden mittels SDS PAGE nach Lämmli (1970) und für Trizin-Gele nach Schägger und Jagow (1987) aufgetrennt. - Der Westernblot Proteintransfer erfolgte mittels Semi-dry-Blotter der Firma BioRad (München) entsprechend den Angaben des Herstellers auf Nitrozellulosemembranen der Firma Amersham Bioscience (UK). Immunoblot Analysen erfolgten nach Angaben der Hersteller. Nachweis von HRP horse-radish-Peroxidase-konjugierten Antikörpern im Immunoblot erfolgte in der Entwicklermaschine M35 X-OMAT Prozessor der Firma Kodak mittels HyperfilmTM-Filmen der Firma Amersham Bioscience (UK). - Quantifizierung von Gelbanden erfolgte mit dem Programm AIDA Image-Analyzer Version 3.10. - Durchflusszytometrische Analysen (FACS) wurden mit Hilfe des FACS Calibur der Firma BD Bioscience (USA) bestimmt und mit dem Software Programm FACS Express V2 ausgewertet. 4.2.2 Kultivierung eukaryotischer Zellen 4.2.2.1 Inkubation und Passagieren von eukaryotischen Zelllinien Sämtliche Zellkulturarbeiten fanden bei sterilen Bedingungen unter einer Sterilwerkbank statt. Zellen wurden in Zellkultur-Schalen oder belüfteten Zellkultur-Flaschen in einem Inkubator bei 37°C, 80% relativer Luftfeuchtigkeit und 5% CO2 kultiviert. Für 293T-, MDBK- und HeLa-Zellen wurde DMEM (Gibco), für MDCK-Zellen MEM (Gibco) und für Jurkat-Zellen RPMI (Gibco) als Kulturmedium unter Zugabe von 5% FKS (PAA) verwendet. Dichte und Morphologie der Zellkulturen wurden regelmäßig am Lichtmikroskop kontrolliert. Bei einer Konfluenz einer Adhäsions-Kultur von ca. 90% wurden die Zellen mit PBS gewaschen, mit 1 ml Trypsin-EDTA abgelöst, in frischem Medium resuspendiert und in einem geeigneten Verhältnis in neue Zellkulturflaschen passagiert. Im Falle der Jurkat-Suspensionszellen wurde als Standard-Passage im Verhältnis 1:10 gesplittet. 4.2.2.2 Kultivierung von primären Zellen Primäre Monozyten und unreife dendritische Zellen wurden im jeweiligen Zellkulturmedium aufgetaut und je nach Verwendungszweck in Zellkulturflaschen (Nunc) oder Multiwell30 Material und Methoden Platten ausgesät (Nunc, Falcon). Primäre Monozyten wurden für mindestens 3 Tage und maximal 10 Tage in Monozytenmedium (DMEM mit 10 % (v/v) humanem Serum, 1% Natriumpyruvat (SIGMA), 170 mM Penicillin und 40 nM Streptomycin) je nach Verwendungszweck kultiviert. Unreife dendritische Zellen wurden in RPMI-Medium (250 U IL-4/ml, 800 U GM-CSF/ml) mit 10% autologem Serum aufgetaut, gewaschen und 24 h später für apoptotische Messungen verwendet. 4.2.2.3 Einfrieren und Auftauen von Zellen Zur Konservierung von Zelllinien wurden Zellen im jeweiligen Medium mit 20% FKS und 10% DMSO resuspendiert und Aliquots von mindestens 1 Mio. Zellen in Cryo-Gefäßen langsam gekühlt und zunächst bei -20°C, nach 24 h bei -80°C eingefroren. Eingefrorene Aliquots wurden schnell bei 37°C aufgetaut und vor der Kultivierung zweifach mit vorgewärmtem DMEM gewaschen. 4.2.2.4 Virusherstellung in Zellkultur Der humanpathogene PR8 Stamm wurde in MDCK-Zellen vermehrt. Dazu wurde eine konfluente 175 cm2 Flasche Zellen mit 15 ml Infektionsmedium (MEM, 1mM MgCl2, 0,9 mM CaCl2, 100 Units/ml Penicillin, 0,1 mg/ml Streptomycin und 0,2% Bovines Albumin) überschichtet. Dazu wurden 1x104 bis 1x105 „plaque forming units“ (pfu) des Virus zupipettiert und für 24 h inkubiert. Nach 24 h wurde der virushaltige Mediumüberstand abgenommen, die toten Zellen abzentrifugiert und verworfen. Der Überstand wurde bei -80°C eingefroren. Die Bestimmung des Virustiters erfolgte ebenfalls mittels Plaque-Assay auf MDCK Zellen. 4.2.2.5 Virusinfektionen von Zellen Vor einer Infektion wurden alle Zellen mit PBS gewaschen, um Serum sowie Zelltrümmer zu entfernen. Die jeweilige Virus-Lösung wurde in PBS (mit 1 mM MgCl2, 0,9 mM CaCl2, 100 Units/ml Penicillin, 0,1 mg/ml Streptomycin und 0,2% Bovines Albumin) aufgenommen bzw. verdünnt. Die Zellen wurden mit 0,5 bis 1 ml Infektionslösung (PBS supplementiert durch 1 mM MgCl2, 0,9 mM CaCl2, 100 Units/ml Penicillin, 0,1 mg/ml Streptomycin und 0,2% Bovines Albumin) überschichtet und für 30 min bei 37°C im Brutschrank infiziert. Im Anschluss wurde die Infektionslösung entfernt und durch serumfreies Medium (jeweiliges Zellmedium supplementiert mit 1 mM MgCl2, 0,9 mM CaCl2, 100 Units/ml Penicillin, 0,1 31 Material und Methoden mg/ml Streptomycin und 0,2% Bovines Albumin) ersetzt. Danach wurden die infizierten Zellen, je nach Verwendungszweck, weiter behandelt. 4.2.2.6 Plaque-Assay und Virustiter Bestimmung Die Anzahl der infektiösen Viruspartikel wurde mittels Plaque-Assay auf MDCK-Zellen bestimmt. Dazu wurde eine logarithmische Verdünnungsreihe der zu untersuchenden Virusüberstände erstellt. Die Viruslösungen für die Verdünnungsreihe wurden in PBS (mit 1 mM MgCl2, 0,9 mM CaCl2, 100 Units/ml Penicillin, 0,1 mg/ml Streptomycin und 0,2% Bovines Albumin) verdünnt. Die MDCK-Zellen wurden in 6-Well Platten mit 500 µl der jeweiligen Virusverdünnung 30 min lang bei 37°C im Brutschrank inkubiert. Danach wurde die Viruslösung entfernt und mit einem Medium-Agar Gemisch (1% Dextran, 3 ml BSA, 85 ml ddH2O, 250 ml 2xMEM, dazu wurden 15 ml 46°C warmer Oxoid-Agar auf 35 ml Medium zugegeben) überschichtet. Humane Influenza-Stämme benötigen außerdem die Zugabe von Trypsin (0,025% v/v), da das Hämagglutinin humanpathogener Influenza Viren tryptisch gespalten werden muss. Die Zellen wurden im Brutschrank für weitere 2-3 Tage inkubiert bis zur sichtbaren Bildung von Plaques. Zuletzt wurden die Plaques mit Neutralrot (in PBS gelöst) oder Coomassie-Blau (0,1% Coomassie-Brilliant-Blue G-250 in 40% Methanol und 10% Essigsäure) angefärbt und ausgezählt. 4.2.3 Apoptosemessungen 4.2.3.1 Annexin-V-Färbung zur FACS-Analyse Um apoptotische Zellen im FACS zu detektieren wurden sie nach Behandlung mit dem zu untersuchenden apoptoseinduzierenden Reagenz bzw. nach einer Transfektion/Infektion mit Hilfe des Vybrant® Apoptosis Assay Kits (Invitrogen) gefärbt. Dazu wurden die behandelten Zellen nach der Inkubation einmal mit eiskaltem PBS und nochmals mit Annexin-Bindepuffer (10 mM HEPES, 140 mM NaCl, 2,5 mM CaCl2, pH 7,4) gewaschen. Danach wurden die Zellen auf 1x106 Zellen/ml mit Bindepuffer eingestellt und 100 µl dieser Suspension mit 5 µl Annexin-V-Lösung (25 mM HEPES, 140 mM NaCl, 1 mM EDTA, pH 7,4, 0,1% BSA, Alexa Fluor 488 Annexin-V) sowie 1 µl Propidiumiodid-Lösung (1mg/ml PI, dH2O) versetzt. Nach 15 minütiger Inkubation (im Dunkeln) wurden 400 µl Bindepuffer je Ansatz zugegeben, die Suspension auf Eis gestellt und im direkten Anschluss am FACS gemessen. 32 Material und Methoden 4.2.3.2 Caspase-3-Aktivitätsmessung Mit Hilfe des Caspase-Glo® 3/7 Assays (Promega) kann die Apoptoseinduktion in Zellkultur standardisiert und schnell gemessen werden. Das Prinzip beruht auf der Lyse der Zellen, wodurch die Effektor-Caspasen-3 und -7 freigesetzt werden und ein Aminoluciferingekoppeltes Substrat, welches bereits im Lysispuffer vorhanden ist und eine DEVDAminosäuresequenz enthält, spalten. Dabei entsteht ein durch eine rekombinante Luciferase umsetzbares Produkt. Bei dieser Umsetzung entsteht Lumineszenz, welche mittels ELISAReader ausgewertet werden kann. Der Ansatz erfolgte im 96-well Format wobei im Falle der Apoptosemessungen in primären Monozyten 2x105 Zellen in 200 µl Medium je well ausgesät wurden. Nach Infektion oder Induktion mit einem apoptotischen Stimulus wurden die Monozyten über Nacht in 100 µl Medium weiter inkubiert und zur Zell-Lyse 100 µl CaspaseGlo®-Lysis/Reaktionspuffer direkt auf das Medium mit den Zellen zugegeben. Nach 1-2 h Lysat-Inkubation bei R.T. erfolgte die Messung am ELISA-Reader bei 590/30 nm. 4.2.3.3 JC1-Färbung 5,5’6,6’-tetrachloro-1,1’,3,3’-tetraethylbenzimidazolylcarbocyaniniodid (JC1) ist ein kationischer Farbstoff, der in den Mitochondrien in Abhängigkeit des Potentials akkumuliert. In apoptotischen Zellen kann am FACS-Gerät ein shift vom Rot-Bereich (590 nm) in den Grün-Bereich (525 nm) beobachtet werden. In proliferierenden Zellen nimmt die rot-Intensität zu. Die zu untersuchenden Zellen wurden auf eine Suspension von 1x106 Zellen/ml eingestellt, mit 10 µg/ml JC1 (Molecular Probes) für 15 min bei 37°C behandelt und 2x mit PBS gewaschen und anschließend am FACS analysiert. 4.2.4 Phosphorylierungsexperimente 4.2.4.1 Herstellung von S10-Extrakten Die Herstellung von S10-Extrakten aus verschiedenen adhärenten Zelllinien wurde, wie zuvor publiziert durchgeführt (Schubert, Schneider et al. 1992). Konfluente Monolayer wurden 2x mit PBS gewaschen und für 2 min bei 37°C abtrypsiniert (0,03% Trypsin, 5 mM EDTA). Die so abgelösten Zellen wurden bei 2000 rpm für 5 min abzentrifugiert, in PBS gewaschen und in S10-Puffer auf Eis resuspendiert (10 mM Tris HCl, pH 7.5, 6 mM MgCl2, 80 mM KCl, 2 mM Dithiothreitol, 0,1% Triton X-100). Das Lysat wurde anschließend bei 10 000 g für 10 min bei 4°C zentrifugiert. Die Überstände wurden aliquotiert und sofort bei -80°C gelagert oder unmittelbar im Ansatz verwendet. 33 Material und Methoden 4.2.4.2 In-vitro-Phosphorylierung Die enzymatische Reaktion zur In-vitro-Phosphorylierung von synthetischem PB1-F2 und überlappenden Peptiden wurde in 20 µl Reaktionspuffer (20 mM Tris HCl, pH 7.5, 10 mM MgCl2, 100 µM CaCl2, 1 mM DTT) in Gegenwart von 2 µg PB1-F2, 2 µCi [γ32]-ATP und 10 mU gereinigter PKC aus Rattenhirn (Calbiochem) oder 5 mU gereinigter CKII (Roche) durchgeführt. Für die Phosphorylierung mit S10-Extrakt wurden 15 µg Zelllysat verwendet und die Proteinkonzentration zuvor mit dem BCA Protein-Assay ermittelt (Pierce). Die PKC Inhibitoren Staurosporin und Bisindolylmaleimid (Calbiochem) wurden in getrennten Ansätzen bis zu einer Endkonzentration von 5 µM zugegeben. Die Reaktion wurde mit der Zugabe des Enzyms gestartet. Die Inkubation erfolgte bei 30°C und wurde nach 20 min durch 2xSDS Probenpuffer abgestoppt. Die Proteine bzw. Peptide wurden in einem 15%igen PAA/SDS-Gel aufgetrennt und für 1 h im Vakuum getrocknet. Abschließend wurde das Gel bei -80°C mit einem BioMax MR X-ray-Film (Kodak) oder mit einer Phosphoimagerplatte (FUJIFILM) exponiert und die Proteinphosphorylierung durch Autoradiographie detektiert. 4.2.4.3 In-vivo-Phosphorylierung Vor der radioaktiven Markierung erfolgte die Transfektion von PB1-F2 exprimierenden Plasmiden bzw. entsprechenden Phsophorylierungsmutanten in 293T Zellen (70-90% Konfluenz) mit einer anschließenden 20 h Inkubationsphase. Die Zellen wurden anschließend für 3 h in phosphatfreiem Medium (Gibco) mit 1% FKS (Dialysiert mit TBS) inkubiert und danach mit Markierungsmedium (DMEM, 200 µCi/ml-orthophosphat (Amersham)) für weitere 4 h behandelt. In den Ansätzen mit PKC-Inhibitoren (Staurosporin (500 nM), Bisindolylmaleimid (10 µM)) wurden diese 15 min vor der radioaktiven Markierung zugegeben, wohingegen der PKC-Aktivator Phorbol-12-Myristat-13-Acetat (PMA (100 ng/ml)) 30 min vor dem Ende der Markierung durch Mediumwechsel zugegeben wurde. Im Falle der IAVPR8-Infektion wurden MDCK-Zellen (70-90% Konfluenz) für 4 h nach der Infektion mit phosphatfreiem Medium inkubiert und danach für weitere 4 h radioaktiv markiert. Nach der radioaktiven Markierung wurden die Zellen 2x mit eiskaltem TBS gewaschen, mittels Zellschaber abgelöst, in 1 ml TBS resuspendiert und anschließend pelletiert (3000 rpm, 4°C, 4 min). Die Pellets wurden in 200 µl RIPA-Puffer (50 mM TrisHCl, 150 mM NaCl, pH 8.5, 1% Nonidet P40, 0,5% Natriumdesoxicholat, 0,1% NatriumSDS, 5 mM EDTA) für 10 min auf Eis lysiert und für 15 min zentrifugiert (14000 rpm, 4°C). Der Überstand wurde für die Immunopräzipitation verwendet. 34 Material und Methoden 4.2.4.4 Immunopräzipitation der radioaktiven Proben Zur Immunopräzipitation wurden 20 µl einer G-Sepharose bead-Lösung 3x mit Triton Waschpuffer (50 mM Tris HCl, pH 7.4, 300 nM NaCl, 0,1% Triton X100, 1 mM PMSF) gewaschen und die beads in 500 µl desselben Puffers resuspendiert, mit 3 µl Serumantikörper gegen das PB1-F2 Gesamtprotein (Seramun) für weitere 1,5 h bei 4°C mittels Drehrad inkubiert und anschließend 3x mit Waschpuffer gewaschen. Das radioaktive Lysat (200 µl) wurde mit der Beadlösung (500 µl) vereinigt und PB1-F2 bei 4°C über Nacht immunopräzipitiert. Danach wurden die beads 2x mit Waschpuffer und 1x mit SDS-DocPuffer (50 mM Tris HCl, pH 7.4, 300 mM NaCl, 0.1% SDS, 0.1% Desoxycholat, 1 mM PMSF) gewaschen. Abschließend wurden die beads in 40 µl 2xSDS Probenpuffer resuspendiert, gebundenes Protein für 10 min bei 70°C denaturiert und der proteinhaltige Überstand in einem 15%igen SDS/PAA-Gel aufgetrennt. Nach dem Trocknen des Gels erfolgte die Detektion der Phosphoproteine wie unter 4.2.4.2 beschrieben. Für Westernblotkontrollen wurden die Proteinkonzentration der Lysate bestimmt (BCA, Pierce) und gleiche Proteinmengen in einem 15%igen SDS/PAA-Gel aufgetrennt, auf Nitrozellulose transferiert und das jeweilige Protein mittels spezifischen Antikörper nachgewiesen. Die Exposition und Detektion erfolgte mittels BioMax MR X-ray-Film (Kodak). 4.2.5 Chemisches Crosslinking Für das chemische Crosslinking wurde sPB1-F2 oder die überlappenden Fragmente PB-(140), PB-(30-70), und PB-(50-87) bei R.T. in PBS mit einem 0.002 bis 2000-fachen molaren Verhältnis der Crosslinker BIS /(Sulfosuccinimidyl)suberate, Pierce), EGS (ethylene-glycoldisuccinate di(N-succinimidyl)ester, Pierce), GA (glutaraldeyhde, Pierce) und DSS (disuccinimidylsuberate, Pierce) inkubiert. Nach 30 min wurde die Crosslinkreaktion durch die Zugabe von Glycin (25 mM) und 10 µl SDS Probenpuffer (2% SDS, 1% βmercaptoethanlol, 10% Glycerol in 65 mM Tris/HCl, pH 6.8) abgestoppt. Die Proben wurden für 5 min bei 95°C denaturiert und über ein 12%iges SDS-Gel aufgetrennt und mittels Westernblot unter Verwendung eines Serum-Antikörpers (Henklein et al. 2005) gegen das Gesamtprotein detektiert. Um die Oligomerisierung mittels Coomassiefärbung zu analysieren wurden 250 µg/ml des sProteins oder der Fragmente bei R.T. in PBS inkubiert. DSS wurde in einem 2- oder 20-fachen molaren Überschuss zugegeben. Nach 30 min wurde die Reaktion mit 25 mM Glycin gestoppt. Die Crosslink-Proben wurden in SDS Puffer (0,2% SDS, 10% Glycerol, 65 mM Tris/HCl, pH 6.8 mit oder ohne 5% β-mercaptoethanol für 5 min bei 55°C gekocht und mittels 15%igem SDS Gel aufgetrennt. Nach der Coomassiefärbung (0,5% 35 Material und Methoden Coomassie Brilliant Blue G-250, 10% Essigsäure, 25% Isopropanol) wurde das Gel entfärbt (25% Methanol, 10% Essigsäure) und analysiert. 36 Ergebnisse 5. Ergebnisse 5.1 Kinetik der PB1-F2 Expression in IAV infizierten Zellen Anfängliche pulse-chase-Experimente anderer Arbeitsgruppen zur Untersuchung der PB1-F2Expression nach einer IAV-Infektion zeigten, dass die Halbwertszeit des Proteins in MDBKLysaten bei nur etwa 30 min liegt und durch die irreversible Inhibition des Proteasoms verlängert werden konnte (Chen, Calvo et al. 2001). Die maximale Proteinsynthese wurde 5 h nach der Infektion detektiert. Ausgehend von diesem Befund wurde untersucht, ob die virale PB1-F2-Expression zellspezifisch ist und das Expressionsmuster möglicherweise in verschiedenen Zelllinien variiert. Hierfür wurden die Epithelzelllinien HeLa und A549 infiziert, wobei die letztere für das Virus permissiv ist und eine produktive Infektion erlaubt (Chen, Calvo et al. 2001), sowie die nicht-permissive Jurkat-CD4+-T-Zelllinie, da PB1-F2 möglicherweise immunzellspezifische Funktionen vermittelt (Lowy 2003; Conenello and Palese 2007). Wie an der Expression der viralen Proteine PB1 und NP zu sehen ist, wurden alle drei Zelllinien mit dem IAVPR8-Laborstamm produktiv und mit gleicher Effizienz infiziert (Abb. 5.1). Abb. 5.1 PB1-F2 Expressionskinetik nach Infektion der Zelllinien Jurkat, HeLa und A549 im Vergleich zu den viralen Proteinen PB1 und NP. Die Zelllinien Jurkat, HeLa und A549 wurden mit IAVPR8 (5 MOI) infiziert und direkt nach der Infektion (0 h) bzw. nach 2, 4, 8 und 24 h mit PBS gewaschen und lysiert. Die Lysate wurden im 12%igen SDS-Gel aufgetrennt und im Westernblot mit einem PB1-F2 spezifischen Serumantikörper analysiert. Das Experiment wurde in Kooperation mit der Arbeitsgruppe Stephan Ludwig am Institut für Molekulare Virologie in Münster durchgeführt. Beide Virusproteine zählen zu den früh exprimierten IAV-Genprodukten und können bereits 2 h nach Viruseintritt detektiert werden. Die PB1-F2-Expression korreliert anfänglich in allen Zelltypen mit der zunehmenden PB1 Synthese, wie sie bereits nach 4 h zu sehen ist. Obwohl die PB1-Expression in der Jurkat und A549 Zelllinie über 24 h relativ konstant bleibt und die 37 Ergebnisse Synthese des viralen Nukleoproteins in allen Zelllinien weiter ansteigt, kann PB1-F2 für 24 h nach der Infektion nicht mehr detektiert werden. Die β-Aktin Kontrolle zeigt auf, dass in den Lysaten zu allen Zeitpunkten vergleichbare Proteinmengen vorhanden waren. 5.2 Untersuchung der pro-apoptotischen Wirkung von exogenem und endogenem PB1F2 in Zellkultur In vorangegangenen Studien wurde berichtet, dass die Präsenz von 50 nM sPB1-F2 im Zellkulturmedium ausreichend war, um nach 4 h Inkubation zytotoxische Effekte in der adhärenten MDBK-Zelllinie zu induzieren (Chen, Calvo et al. 2001). Auf diesem Befund basieren die folgenden Experimente. 5.2.1 Inkubation von Epithelzelllinien mit sPB1-F2 und Analyse mittels Annexin-VFärbung Zur Untersuchung einer möglichen exogenen Funktion von PB1-F2 wurde ein über Festphasen-Peptidsynthese hergestelltes, synthetisches Peptid verwendet, welches hochrein und in biologisch aktiver Form erhältlich war (Abb. 5.2.1A) (Chanturiya, Basanez et al. 2004; Henklein, Bruns et al. 2005). Mit einer Sequenz von 87 A.s. und einem Molekulargewicht von 11 kD entspricht das sPB1-F2 dem vom IAVPR8-exprimierten Wildtyp-Protein und zeigt die gleichen biochemischen Eigenschaften wie das virale Protein (Henklein, Bruns et al. 2005). Vorausgegangene Untersuchungen zeigten, dass die Präsenz von 50 nM sPB1-F2 im Zellkulturmedium zytotoxische Effekte in MDBK-Zellen und 300 nM sPB1-F2 Cytochromc-Freisetzung in HeLa-Zellen induziert (Chen, Calvo et al. 2001). Auf diesen Arbeiten basierend, wurden HeLa Zellen für 4 h mit 300 nM sPB1-F2 inkubiert und die Zellen zu verschiedenen Zeitpunkten nach der Inkubation mit dem Apoptosemarker Annexin-V gefärbt und mittels FACS analysiert (Abb. 5.2.1B). Diese Methode erlaubt eine präzise Angabe des prozentualen Anteils aller apoptotischer und nekrotischer Zellen, die durch Propidiumiodid(PI)-Kofärbung detektiert wurden. Wie in Abbildung 5.2.1B zu sehen ist, zeigten die mit exogenem sPB1-F2 inkubierten HeLa-Zellen im Vergleich zur unbehandelten Kontrolle keine prozentuale Zunahme an apoptotischen Zellen, wohingegen eine mit UV-Strahlung induzierte Positivkontrolle einen Teil der Zellen bereits direkt nach der vierstündigen Inkubationsphase (t = 0 h) zur Apoptose stimulierte. Da apoptotische Prozesse, je nach Stimulus, bis zum Einsetzen der zellulär messbaren Induktion zeitlich stark variieren können, wurde die Messreihe bis zu 50 h fortgesetzt. Eine Zunahme an apoptotischen Zellen in dem mit sPB1-F2 inkubierten Ansatz konnte jedoch in diesem Zeitraum nicht gemessen werden. Die UVinduzierten Kontrollzellen waren bereits nach 15 h vollständig apoptotisch oder nekrotisch. 38 Ergebnisse Um den Anteil des an die Zelloberfläche gebundenen bzw. aufgenommenen sPB1-F2Proteins nachzuweisen, wurden parallel zu jedem Zeitpunkt Zelllysate erstellt und sPB1-F2 mit einem spezifischen Serumantikörper (Henklein, Bruns et al. 2005) im Westernblot nachgewiesen (Abb. 5.2.1C). Sowohl das sPB1-F2-Monomer (11 kD) als auch das Dimer (21 kD) konnten noch bis zu 5 h nach dem Entfernen des Proteins durch Mediumwechsel nachgewiesen werden und waren noch nach 15 h in Spuren präsent. Abb. 5.2.1 Kinetik und FACS-Analyse von sPB1-F2 inkubierten HeLa-Zellen. (A) Qualitative Kontrolle von 2 µg (s)PB1-F2 durch Coomassie Färbung. (B) 1x106 HeLa-Zellen wurden für 4 h mit sPB1-F2 inkubiert, 2x mit PBS gewaschen und zur anschließenden FACS-Analyse Annexin-V gefärbt. Die Zahl der apoptotischen Zellen wurde in einem Zeitraum bis zu 50 h nach der Inkubation gemessen und in Prozent angegeben. (C) Für jeden Zeitpunkt nach der Inkubation mit sPB1-F2 wurden 1x105 Zellen 2x mit PBS gewaschen und in SDS-Probenpuffer lysiert. Anschließend erfolgte die Auftrennung in einem 15%igen SDS-Gel, und PB1-F2 wurde mittels serumspezifischenAntikörper im Westernblot detektiert. Dieser Befund spricht dafür, dass die exogene Stabilität von sPB1-F2 deutlich größer ist als die beschriebene Halbwertszeit des endogenen, viralen Proteins von nur 30 min (Chen, Calvo et al. 2001), was eine wichtige Voraussetzung für ein funktionell exogen agierendes Virusprotein wäre. Dennoch war die alleinige Präsenz von sPB1-F2 im Zellkulturmedium nicht ausreichend, um zytotoxische Effekte in HeLa-Zellen zu induzieren. Im Rahmen dieser Arbeit wurde festgestellt, dass eine Erweiterung der experimentellen Bedingungen auf erhöhte sPB1-F2-Konzentrationen (bis zu 10 µM), permanente Präsenz des sPB1-F2-Proteins im Medium (bis zu 72 h) und die Inkubation verschiedener Epithelzelllinien (MDBK, MDCK, 293T) sowie primärer Zellen (Monozyten, dendrititsche Zellen) in keiner detektierbaren Apoptoseinduktion resultierten (Daten nicht gezeigt). Demnach kann davon ausgegangen 39 Ergebnisse werden, dass exogenes PB1-F2 nicht ausreicht, um zytotoxische Effekte in Zellkultur zu generieren. 5.2.2 Exogenes sVpr, aber nicht sPB1-F2, induziert Apoptose in T-Lymphozyten Neuere Ergebnisse sprechen für eine immunmodulatorische Bedeutung des PB1-F2-Proteins vor allem in hochpathogenen IAV-Isolaten (Conenello and Palese 2007). Eine Hypothese geht davon aus, dass PB1-F2 Immunzellen im Kontext einer akuten Infektion eliminiert und dies möglicherweise exogen vermittelt wird, indem das Protein von einer infizierten Zelle freigesetzt wird und Nachbarzellen transduziert, wie es bereits für das akzessorische VprProtein bekannt ist (Lowy 2003; Bruns, Studtrucker et al. 2007). Um zu klären, ob exogenes PB1-F2 spezifische Lymphozyten-Zytotoxizität vermittelt, wurden Jurkat-T-Zellen für 8 bzw. 24 h mit sPB1-F2 oder sVpr inkubiert (Abb. 5.2.2.1). Als Positivkontrolle wurden die Jurkatzellen mit dem chemischen Stimulus Etoposid in die Apoptose überführt. Während der prozentuale Anteil der apoptotischen und nekrotischen Zellen in der unbehandelten Kontrolle und in den mit sPB1-F2 inkubierten Zellen bei 4-6% konstant blieb, konnte in den mit sVpr behandelten Zellen ein deutlicher zytotoxischer Effekt mit einem Anteil von 18% apoptotischer Zellen nach 8 h detektiert werden (Abb. 5.2.2.1). Kontrolle sPB1-F2 Data.001 10 2 10 1 88,77% 10 0 10 3 10 2 10 1 0,05% 88,02% 4,58% 10 1 2 10 FL1-H 10 3 10 7,02% 4 10 0 1 3 10 2 10 1 89,50% 10 0 10 4 10 3 10 2 10 1 4,09% 10 1 2 10 FL1-H 10 3 3 10 2 10 1 18,65% 62,34% 10 4 10 0 2 10 FL1-H 10 3 10 6,50% 89,35% 4 10 0 10 4 10 3 10 2 10 1 1 4 10 3 10 2 10 1 0,13% 1 2 10 FL1-H 10 3 10 13,69% 27,80% 18,84% 10 4 10 0 58,38% 10 1 2 10 FL1-H 10 3 10 4 10 0 10,98% 10 4 10 3 10 2 10 1 14,23% 10 1 2 10 FL1-H 10 3 10 4 Data.010 0,06% 74,73% 4,04% 10 10 Data.008 0,11% FL2-H 10 6,31% Data.004 0,17% Data.009 0,10% FL2-H FL2-H 24 h 4 10 4,91% 10 Data.007 10 10 FL2-H 3 6,64% Data.005 4 FL2-H 10 0,01% 4 Etoposid sVpr Data.006 10 FL2-H 4 FL2-H FL2-H 8h 10 2 10 FL1-H 10 3 10 4 0,05% 37,21% 8,12% 10 0 54,62% 10 1 2 10 FL1-H 10 3 10 4 nekrotische Zellen apoptotische Zellen Abb. 5.2.2.1 Annexin-V-Färbung von Jurkat-T-Zellen nach Inkubation mit sVpr oder sPB1-F2. Jurkat-T-Zellen wurden für 8 bzw. 24 h mit 3 µM sPB1-F2 oder sVpr inkubiert, in PBS gewaschen und mit dem Apoptosemarker Annexin-V bzw. mit Propidiumiodid zur Detektion der nekrotischen Population inkubiert. Der chemische Stimulus Etoposid (60 µM) diente als Positivkontrolle. 40 Ergebnisse Um auszuschließen, dass die PB1-F2-vermittelte Apoptoseinduktion zu einem späteren Zeitpunkt verläuft, wurden die Zellen bis zu 72 h mit sPB1-F2 bzw. sVpr inkubiert (Abb. 5.2.2.2). Es zeigte sich, dass exogenes PB1-F2 zu keinem Zeitpunkt zu einer signifikant gesteigerten Zytotoxizität im Vergleich zu den unbehandelten Kontrollzellen beigetragen hat. Wie zu erwarten, nimmt die durch sVpr vermittelte Apoptose zeitabhängig ab, da das Protein im Gegensatz zu starken Stimuli wie UV-Strahlung oder der Chemikalie Etoposid nicht in allen Zellen Apoptose induziert und die sVpr-Stabilität im Zellkulturmedium zeitlich limitiert ist (Sherman, Schubert et al. 2002). 5.2.2.2 72 h-Inkubation von Jurkatzellen mit sPB1-F2. Jurkat-Zellen wurden bis zu 72 h mit sVpr oder sPB1-F2 inkubiert (3 µM) und die Apoptoseinduktion durch Annexin-V-positive Zellen am FACS gemessen. 5.2.3 Die Expression von endogenem PB1-F2 in 293T-Zellen hat keinen Einfluss auf die Caspase-3-Aktivität PB1-F2 wurde usrsprünglich als pro-apoptotisches Protein beschrieben, das hauptsächlich in den Mitochondrien von IAV-infizierten oder transient transfizierten Zellen lokalisiert ist und dort morphologische Veränderungen der tubulären Mitochondrienstruktur zu einer sphärischen Form hin induziert und zu gesteigerter Cytochrom-c-Freisetzung beiträgt (Chen, Calvo et al. 2001; Zamarin, Garcia-Sastre et al. 2005). Damit ist PB1-F2 das einzige bisher bekannte Influenza Protein, welches die sogenannte intrinsische apoptotische Signalkaskade aktiviert (Lowy 2003). Ein Schlüsselenzym zur Messung apoptotischer Induktion nach einer IAV-Infektion ist die Effektorcaspase-3, welche sowohl durch die extrinsische, rezeptorvermittelte (z.B. Fas-Ligand) als auch intrinsische, mitochondirale Kaskade aktiviert wird (Ludwig, Pleschka et al. 2006). Ein zelluläres Substrat der aktiven Caspase-3 ist die Poly-ADP-Ribose-Polymerase (PARP), welche von der Caspase gespalten wird und daher 41 Ergebnisse als spezifischer Apoptosemarker Anwendung findet (Nicholson, Ali et al. 1995). Um zu untersuchen, ob zellulär exprimiertes PB1-F2 die Caspase-3-Aktivität stimuliert, wurden 293T-Zellen mit Plasmiden transfiziert, die entweder für PB1-F2 oder zur Kontrolle das virale PB1-Protein exprimieren. Abb. 5.2.3 Zellulär exprimiertes PB1-F2 ist nicht ausreichend, um apoptotische Effekte in 293TZellen zu induzieren. (A) 24 h nach transienter Transfektion von 293T-Zellen mit Plasmiden, die für PB1-F2 oder die virale Polymerase PB1 codieren, wurden die Lysate in einem 12%igen SDS-Gel aufgetrennt und mit spezifischen Antikörpern im Westernblot analysiert. (B) In den Lysaten von 1x105-Zellen je transfiziertem Ansatz wurde durch ein spezifisches Substrat (Z-DEVD) die Caspase-3-Aktivität luminometrisch ermittelt. Die Apoptoseinduktion wurde durch PARP-Spaltung im Westernblot analysiert (Abb. 5.2.3). PB1-F2 konnte in 293T-Zellen exprimiert und mit einem spezifischen Serumantikörper (Henklein, Bruns et al. 2005) im Vergeich zu einer MOCK-transfizierten Kontrolle deutlich detektiert werden. Interessanterweise war die Transfektion der für PB1 kodierenden Plasmid DNA-Sequenz bereits ausreichend, um die Expression von PB1-F2-downstream nach dem zuvor beschriebenen Mechanismus der alternativen Startcodon-Erkennung zu initiieren (siehe Einleitung). Ein Spaltprodukt für PARP (c-PARP) mit einem erwarteten Molekulargewicht von 87 kD konnte nur in den mit Staurosporin bzw. Etoposid behandelten Zellen detektiert werden, jedoch nicht in den transfizierten Zellen, wobei die Sensitivität der Methode in diesem System aufgrund des schwachen Bandensignals der apoptotischen Positivkontrollen nicht zufriedenstellend war. Deshalb wurden die transfizierten Zellen parallel in einem kommerziellen Caspase-3-Luziferase-Aktivitätsassay untersucht. Im Vergleich zu den unbehandelten Kontrollzellen konnte in keinem der transfizierten Ansätze eine gesteigerte Caspaseaktivität gemessen werden (Abb.5.2.3B). Diese Ergebnisse stimmen mit später 42 Ergebnisse publizierten Daten überein, wonach endogen exprimiertes PB1-F2 alleine nicht in der Lage ist, Apoptose in Epithelzellen zu induzieren (Zamarin, Garcia-Sastre et al. 2005). 5.2.4 Exogenes sPB1-F2 hat keinen Einfluss auf die apoptotische Sensibilisierung verschiedener Zelllinien Nach der Transfektion der Eptihelzelllinien 293T und A549 konnte gezeigt werden, dass endogenes PB1-F2 die Effekte zellulärer pro-apoptotischer Stimuli verstärkt (Zamarin, Garcia-Sastre et al. 2005). Um zu überprüfen, ob extrazelluläres PB1-F2 gleichfalls zu einer gesteigerten Apoptoserate beiträgt, wurden HeLa-Zellen für 5 h mit sPB1-F2 präinkubiert und danach UV- bestrahlt. A M1 C ount 120 M2 100 80 M2 M2 60 40 20 0 0 1 10 10 B ´ 2 10 FL1-H 3 4 10 10 C 14, 000 35000 12, 000 30000 10, 000 25000 8, 000 20000 6, 000 15000 4, 000 10000 2, 000 5000 0, 000 0 Kontr ol l e sPB1-F2 [10 µM] STS[0,5 µM] Kont rolle STS[0,5 µM] +sPB1F2 [10 µM] Et oposid [ 100 Et oposid [ 100 µM] UV [ 200 mJ] UV [ 200 mJ] + µM] + sPB1-F2 sPB1-F2 [ 10 [ 10 µM] µM] Abb. 5.2.4 Exogenes sPB1-F2 hat keinen verstärkenden Einfluss auf apoptotische Stimuli. (A) 1x106 HeLa-Zellen wurden mit oder ohne sPB1-F2 (10 µM) inkubiert, UV-bestrahlt (250mJ/cm2) und nach 6 h mit dem Mitochondrienpoteinial-sensitiven Farbstoff JC1 am FACS gemessen. Die UVbehandelten Zellen (roter Graph) und die Zellen, die zusätzlich mit sPB1-F2 behandelt wurden (blauer Graph), zeigen keine signifikanten Unterschiede. (B) 5x104 Jurkat-Zellen wurden für 12 h mit sPB1F2 (10µM) inkubiert und anschließend mit 0,5 µM STS behandelt oder ohne den Stimulus inkubiert. 6 h nach der Induktion wurden die Zellen lysiert und die Caspase-3-Aktivität in den Lysaten gemessen. (C) Nach sPB1-F2 Inkubation (wie in B) wurde die Apoptose von 5x104-MDCK-Zellen entweder mit Etoposid [100 µM] oder UV-Strahlung [200 mJ/cm2] induziert und nach weiteren 6 h die Caspase-3Aktivität bestimmt. 43 Ergebnisse Nach weiteren 4,5 h erfolgte die Messung mit dem Mitochondrienpotential-sensitiven JC1Farbstoff mittels FACS-Analyse (Abb. 5.2.4A). Die UV-bestrahlten Zellen zeigen für 5 h nach der Induktion einen deutlich einsetzenden shift in den Grünkanal für 24% der Gesamtpopulation, der eine Destabilisierung des mitochondrialen Potentials dieser Zellen anzeigt (roter Graph, M2) und bei den unbehandelten Kontrollzellen nicht vorhanden war (schwarzer Graph, 2%). Dabei konnte kein signifikanter Unterschied zwischen den nur UVbestrahlten HeLa Zellen und den Zellen, die sowohl UV-bestrahlt als auch mit sPB1-F2 inkubiert wurden (blauer Graph, 31% der Population) festgestellt werden. Um weitestgehend auszuschließen, dass eine mögliche exogene Sensibilisierung durch PB1-F2 zellspezifisch vermittelt wird, wurden Jurkat- bzw. MDCK- Zellen für 10 h mit sPB1-F2 präinkubiert, anschließend mit den Apoptosestimuli Staurosporin (STS) oder Etoposid behandelt und die Caspase-3-Aktivität bestimmt (Abb. 5.2.4B). In beiden Ansätzen konnte keine Aktivitätssteigerung durch die Präsenz von 10 µM sPB1-F2 im Zellkulturmedium nachgewiesen werden, wodurch erneut bestätigt wurde, dass exogenes sPB1-F2 für die Induktion zytotoxischer Effekte nicht relevant ist. 5.2.5 PB1-F2 verstärkt die virusinduzierte Apoptose in primären humanen Monozyten Nachdem in vorangegangenen Arbeiten durch Annexin-V-Färbung gezeigt werden konnte, dass die Apoptoserate nach einer Infektion mit Wildtyp-IAVPR8 in der humanen monozytären Zelllinie U937 um etwa 40% höher liegt als bei einer Virusmutante, die für PB1-F2 deletiert ist (Chen, Calvo et al. 2001), sollte untersucht werden, ob sich dieses Phänomen auch in primären, elutrierten Monozyten von gesunden Spendern reproduzieren lässt. Hierfür wurden die Monozyten entweder mit dem Wildtyp-IAVPR8 infiziert, oder mit einer Deletionsmutante IAVPR82xΔF2, die kein Startcodon zur Expression von PB1-F2 besitzt und zusätzlich ein Stopcodon nach 12 Aminosäuren innerhalb des +1 überlappenden Leserahmens von PB1 integriert hat (Mazur, Anhlan et al. 2008). Die Caspase-3-Aktivität der Zelllysate wurde für 4, 8, 16 und 20 h nach der Infektion gemessen. Es konnte festgestellt werden, dass die von beiden Viren induzierten apoptotischen Effekte bereits nach 16 h deutlich detektierbar sind, was mit früheren Publikationen übereinstimmt, die eine messbare Aktivität der Caspase-3 für einen Zeitraum von 16 h bis 30 h beschreiben (Lowy 2003) (Abb. 5.2.5A). Im Vergleich dazu erfolgte die einzige im Westernblot detektierbare PB1-F2-Expression nach 8 h, was mit dem Peak in anderen Zelltypen übereinstimmt (vgl. Abb. 5.1), wohingegen das PB1-F2-defiziente Virus wie erwartet keine Expression aufweist. Die Differenz der relativen Caspase-3-Aktivität des Zelllysates der Wildtyp-Virus-infizierten Zellen im Vergleich zum Lysat der 44 Ergebnisse Virusmutante, welche für 16 h bzw. 20 h nach der Infektion gemessen wurde, entspricht in etwa dem Anteil der zuvor durch FACS-Analysen prozentual ermittelten gesteigerten Anzahl apoptotischer Monozyten von 30% - 40% (Chen, Calvo et al. 2001). Dieses Ergebnis verdeutlicht, dass das PB1-F2 defiziente Virus weniger Apoptose in primären Monozyten induziert als das Wildtyp-Virus. Abb. 5.2.5 Die Induktion der Caspase-3-Aktivität ist in PB1-F2-defizienten Viren reduziert. (A) Primäre humane Monozyten (2x105 Zellen) wurden mit Wildtyp-Virus (IAVPR8) oder einer PB1-F2-deletierten Mutante (IAVPR82xΔF2) infiziert (MOI 5) und die Caspase-3-Aktivität der Lysate zu den angegebenen Zeitpunkten nach der Infektion luminometrisch gemessen. (B) Westernblotkontrolle der Infektionskinetik. Die PB1-F2 Expression konnte nur für 8 h nach der Infektion nachgewiesen werden. 5.3 Das IAV-Protein PB1-F2 wird von der Proteinkinase C phosphoryliert Ursprünglich wurde PB1-F2 als ein Protein beschrieben, das nach der Infektion von [35S]Met-markierten MDBK-Zellen und anschließender Immunopräzipitation in einem Muster von drei dicht nebeneinander lokalisierten Proteinbanden detektiert werden kann (Chen, Calvo et al. 2001). Auf dieser Beobachtung basieren die nachfolgenden Untersuchungen, um zu klären, ob PB1-F2 durch posttranslationale Modifikationen, wie z.B. Phosphorylierung, modifiziert wird und welche Kinasen in diesen Prozess involviert sind. 45 Ergebnisse 5.3.1 PB1-F2 enthält mehrere potentielle Phosphorylierungsstellen mit PKC- und CK2Konsensussequenzen Die Analyse der PB1-F2-Sequenz des IAV-Isolates A/Puerto Rico/8/34(H1N1) (IAVPR8) wurde in silico mit dem Programm „NetPhos“ erstellt. Die Phosphorylierungsstellen in Position Thr-18, Thr-27, Ser-35 und Ser-84 besitzen die größte vorausgesagte Phosphorylierungswahrscheinlichkeit von insgesamt 13 potentiellen Phosphoaminosäuren (Ser/Thr/Tyr) innerhalb der Sequenz (Abb. 5.3.1, rechter Abschnitt). Der prediction score (Pscore) für jede der möglichen Phosphorylierungsstellen liegt zwischen 0 (0%) und 1 (100%) und wird im Kontext der die Phosphorylierungsstelle umgebenden Aminosäuresequenz kalkuliert, wobei berücksichtigt werden muss, dass vorhergesagte Phosphorylierungsstellen nur relevant sind, wenn ihr Pscore > 0,5 ist (Blom, Gammeltoft et al. 1999). Abb. 5.3.1 In-silico-Sequenzanalyse von PB1-F2 unter Darstellung der potentiellen Phosphorylierungsstellen. Mehrere spezifische Erkennungsmotive für die PKC und eines für die CKII befinden sich inerhalb der Proteinsequenz. Der rechte Abschnitt zeigt die numerische Wahrscheinlichkeit (Pscore) mit der jede der identifizierten Phosphorylierungsstellen innerhalb einer spezifischen Konsensussequenz tatsächlich phosphoryliert wird. Weiterhin ist es möglich, dass eine Phosphorylierungsstelle von mehreren Kinasen phosphoryliert wird (Blom, Sicheritz-Ponten et al. 2004). Zur Analyse der potentiellen Kinasen-Konsensusmotive innerhalb der PB1-F2-Sequenz wurde das Programm „PROSITE“ verwendet (Abb. 5.3.1). Dabei wurden insgesamt drei relevante PKC- Phosphorylierungsstellen für die A.s. in Position 18 (Thr), 27 (Thr) und 35 (Ser) identifiziert, welche auf dem minimalen Konsensus-Motiv S/TXK/R basieren (Woodgett, Gould et al. 1986) und ein C-terminales S/KH/E-Motiv für die Casein-Kinase-2 (CK-2). Nach neuesten Strukturanalysen besitzt PB1-F2 zwei kleinere α-Helices im N-Terminus und ein große αHelix von A.s. Ile-53 bis Lys-85 im C-Terminus (vgl. Abb. 2.6.2), welche die bisher bekannten funktionellen Regionen des Proteins umfasst (Bruns, Studtrucker et al. 2007). Die potentiellen Phosphorylierungsstellen befinden sich in der unstrukturierten Region von PB1F2, was frühere Beobachtungen bestätigt, dass spezifische Kinasen-Erkennungsmotive häufig in den unstrukturierten Bereichen eines Proteins vorliegen, aufgrund der idealen sterischen Zugänglichkeit für die Bindetasche der jeweiligen Kinase (Roach 1991; Blom, Gammeltoft et al. 1999). 46 Ergebnisse 5.3.2 sPB1-F2 wird von der Protein-Kinase-C (PKC) in-vitro-phosphoryliert Nachdem die PKC und CK-2 als potentielle Kinasen der PB1-F2-Phosphorylierung in silico identifiziert wurden, sollten In-vitro-Experimente aufzeigen, ob diese Vorhersagen tatsächlich zutreffen. Hierfür wurden synthetisch hergestellte PB1-F2 Proteine vom IAVPR8-Isolat (Henklein, Bruns et al. 2005) oder vom Spanischen-Grippe-Isolat A/Brevig Mission/1/18 (H1N1) (IAVSF2) (Roder, Bruns et al. 2008) verwendet und mit kommerziell erhältlicher, aufgereinigter PKC bzw. CK-2 in Gegenwart von [γ32]-ATP inkubiert (Abb. 5.3.2.1A). Während das sPB1-F2 beider Isolate deutlich von der PKC phosphoryliert wird, zeigt sich für die Caseinkinase unter gleichen Bedingungen nur ein schwaches Phosphorylierungssignal, obwohl das Enzym vollkommen aktiv ist, was durch die Autophosphorylierung seiner regulatorischen und katalytischen Untereinheiten (α+β-UE) deutlich zu sehen ist (Bodenbach). Die PKC-Phosphorylierung erfolgte mit aufgereinigtem Rattenhirnextrakt, welches hauptsächlich die konventionellen PKC-Isoformen α, β1, β2 und γ enthält (Kikkawa, Go et al. 1986). A B C Abb. 5.3.2.1 Das sPB1-F2-Protein wird von der PKC in vitro phosphoryliert und die Phosphorylierung wird durch PKC-Inhibitoren deutlich reduziert. (A) sPB1-F2, welches entweder der Sequenz des IAVPR8- oder IAVSF2-Isolates entspricht, wurde verwendet, um die 32 Phophorylierung in Gegenwart von gereinigter PKC aus Rattenhirn oder der CK-2 und [γ ]-ATP zu untersuchen. (B) Phosphorylierung von sPB1-F2 durch HeLa Zellextrakt (S10-Extrakt). Für die invitro-Inhibition der PKC wurden verschiedene Konzentrationen der Inhibitoren STS umd BIM eingesetzt. (C) Die PB1-F2-Phosphorylierung mittels S10-Extrakt wurde durch einen Kontrollinhibitor bis zu 10 µM nicht reduziert. 47 Ergebnisse Die In-vitro-Experimente wurden weiterführend auch mit zellulären HeLa-Extrakten (S10Extrakte) vollzogen (Schubert, Schneider et al. 1992). Die Inkubation von sPB1-F2 mit [γ32]ATP resultierte in der deutlichen Phosphorylierung von PB1-F2, die in Abhängigkeit der PKC-Inhibitorenkonzentration von Staurosporin (STS) und Bisindolylmaleimid (BIM) blockiert wurde (Abb. 5.3.2.1B). Dabei muss berücksichtigt werden, dass Zellextrakte ein Gemisch aus allen zellulärer Kinasen darstellen und PB1-F2 möglicherweise noch mit anderen Kinasen interagiert, so dass eine völlige Inhibition mit PKC-spezifischen Inhibitoren unter diesen Bedingungen nicht erzielt werden kann. Obwohl STS ein sehr potenter Inhibitor aller PKC-Isoformen ist (Tamaoki, Nomoto et al. 1986), können auch andere Kinasen inhibiert werden, wie z.B. die Protein-Kinase-A (PKA) oder die virale p60-src-kinase (p60vsrc) (Nakano, Kobayashi et al. 1987; Ruegg and Burgess 1989). Im Gegensatz dazu ist BIM ein selektiverer PKC-Inhibitor, der vor allem für die konventionellen PKC Isoformen sensitiv ist (Toullec, Pianetti et al. 1991; Gescher 1998). Dass die Phosphorylierung von PB1-F2 vornehmlich von Serin- oder Threoninkinasen vermittelt wird und Tyrosinkinasen nicht beteiligt sind, wird dadurch bestätigt, dass BIM bereits ab einer Konzentration von 0,5 µM nachweislich zur Inhibition der PB1-F2-Zellextrakt-Phosphorylierung beiträgt (Abb. 5.3.2.1B) und dieser Inhibitor erst ab einer 100fach höheren Konzentration unspezifisch Tyrosinkinasen inhibiert (Toullec, Pianetti et al. 1991). Interessanterweise zeigt die Kontrolle mit einem sensitiven Inhibitor der Phosphoinositol-3- Kinase (PI3-Kinase), die ebenfalls im Kontext der IAV-Infektion aktiviert wird (Ludwig, Pleschka et al. 2006; Ehrhardt, Wolff et al. 2007), dass die S10-Extrakt-vermittelte PB1-F2-Phosphorylierung selbst für mikromolare Konzentrationen des PI3-sensitiven Inhibitors Wortmannin nicht beeinträchtigt wird (Abb. 5.3.2.1C), wohingegen Staurosporin die Phosphorylierung durch das S10-Extrakt vollständig blockiert. Die primären Wirtszellen der Influenza-A-Viren im Menschen sind die alveolaren Epithelzellen der Lunge (Suzuki, Ito et al. 2000; Wright 2001). Daher wurden A549Lungenepithelzellen mit Zelllinien verglichen, die gleichsam permissiv für IAV sind und eine produktive Replikation erlauben (Chen, Calvo et al. 2001), und untersucht, ob sich in vitro Unterschiede im PB1-F2-Phosphorylierungsmuster zeigen. Wie in Abbildung 5.3.2.2 zu sehen, wurde PB1-F2 von allen hier verwendeten Epithelzellextrakten phosphoryliert. Am effizientesten erfolgte die Phosphorylierung mit dem Extrakt aus A549-humanen Lungenepithelzellen, den eigentlichen Zielzellen des Virus. Die Westernblotkontrolle (Abb. 5.3.2.2B) zeigte, dass vergleichbare Mengen sPB1-F2 in allen Ansätzen vorhanden sind. Die 48 Ergebnisse A B Abb. 5.3.2.2 PB1-F2 wird von den Extrakten verschiedener Zelllinien phosphoryliert. (A) S10Extrakte verschiedener Zelllinien (15 µg je Ansatz) wurden in vitro zusammen mit sPB1-F2 und 32PATP inkubiert und mittels Autoradiographie detektiert. (B) Die Westernblottkontrolle mit einem spezifischen PB1-F2-Serumantikörper bestätigt, dass in allen Ansätzen vergleichbare Mengen an sPB1-F2 vorhanden waren. Expression und Verteilung der verschiedenen PKC-Isoformen kann stark zwischen verschiedenen Zelltypen und Geweben schwanken. Einige Isoforme wie z.B. die PKCα werden ubiquitär exprimiert, wohingegen andere, z.B. die PKCγ extrem gewebsspezifisch sind (Webb, Hirst et al. 2000). Die effiziente PB1-F2-Phosphorylierung durch A549-Extrakt steht im Einklang mit vorangegangenen Publikationen, welche die PKCα als die dominante Isoforme in A549-Zellen beschrieben haben (Levesque, Dean et al. 1997) und der bereits zuvor angesprochenen Tatsache, dass sPB1-F2 durch die überwiegend konventionellen Isoformen des Rattenhirns effizient phosphoryliert wird. 5.3.3 PB1-F2 wird in transfizierten 293T-Zellen phosphoryliert Um die Frage zu klären, ob PB1-F2 auch in vivo phosphoryliert wird, wurden 293T-Zellen mit einem Expressionskonstrukt, welches das pb1-f2-Gen exprimiert, transient transfiziert. Anschließend wurden die Zellen mit [32P]-Orthophosphat radioaktiv markiert und PB1-F2 mit einem spezifischen Serumantikörper immunopräzipitiert (Henklein, Bruns et al. 2005). Wie in Abbildung 5.3.3 (Reihe 2) deutlich zu sehen ist, zeigt sich eine radioaktive Proteinbande mit dem erwarteten Molekulargewicht von 11 kDa in den PB1-F2-exprimierenden 293T-Zellen, jedoch nicht in der MOCK-transfizierten Kontrolle (Reihe 1). Um zu bestätigen, dass es sich hierbei tatsächlich um PB1-F2 handelt, und um die Menge an exprimierten PB1-F2 in Relation zum Signal des radioaktiven Proteins setzen zu können, wurde eine zusätzliche 49 Ergebnisse Westernblot-Kontrolle erstellt (siehe Unterhalb). In weiteren Experimenten wurde untersucht, ob die in-vivo-Phosphorylierung von PB1-F2 im Kontext der PKC-Aktivität steht. Hierfür wurden die transfizierten 293T-Zellen mit Reagenzien behandelt, welche die PKC entweder aktivieren (Phorbol-Myristyl-Acetat, PMA) oder inhibieren (BIM, STS, vgl. 5.3.2). Nach 30 min Inkubation mit PMA konnte die PB1-F2-Phosphorylierung verdoppelt werden (nach densitometrischer Analyse mit dem AIDA Software-Programm). Im Gegensatz dazu war das Phosphorylierungssignal in Gegenwart der Inhibitoren BIM bzw. STS deutlich reduziert. Diese Daten bestätigen auch die zuvor in vitro ermittelte Phosphorylierung von PB1-F2 durch die PKC, von der bekannt ist, dass sie nach einer IAV-Infektion aktiviert vorliegt (Kurokawa, Ochiai et al. 1990; Sieczkarski, Brown et al. 2003). A B Abb. 5.3.3 PB1-F2 wird nach transienter Transfektion phosphoryliert, und die Signalintensität kann durch PMA gesteigert oder mit PKC-spezifischen Inhibitoren reduziert werden. (A) Autoradiographie eines 293T-Zell-Lysates für 24 h nach der Transfektion mit einem Kontrollvektor (Reihe 1) oder einem PB1-F2-Expressionsvektor (pPB1-F2). Die Zellen wurden für 4 h vor der Lyse 32P radioaktiv markiert und PB1-F2-immunopräzipitiert (IP). Die Westernblot-Kontrolle der IP-Proben ist unterhalb zu sehen. (B) Die Signalintensität der Autoradiographie von PB1-F2-transfizierten unbehandelten Zellen (Reihe 1) wurde mit Zellen, die entweder PMA (100ng/ml, Reihe 2) oder mit den Kinaseinhibitoren BIM (10 µM, Reihe 3 bzw. STS (500 nM, Reihe 4) während der Radioaktiven 32P-Markierung behandelt wurden, verglichen. Die Westernblot-Kontrolle der IP-Proben unterhalb zeigt, dass die Proteinexpression von PB1-F2 durch die Präsenz des chemischen Aktivators oder der Inhibitoren nicht beeinträchtigt wurde. 50 Ergebnisse 5.3.4 PB1-F2 wird an den PKC-Phopshorylierungsstellen Serin-35 und Threonin-27 in vitro phosphoryliert Nachdem gezeigt wurde, dass PB1-F2 ein Phosphoprotein ist, galt es, die relevanten Phosphorylierungsstellen innerhalb des Proteins zu ermitteln. Hierfür wurden 15 synthetische Peptide mit einer Länge von 20 A.s. (20mere) verwendet, welche die gesamte Sequenz von PB1-F2 umfassen (Abb. 5.3.4) (Henklein, Bruns et al. 2005). Jedes einzelne Fragment wurde in vitro mit S10-Extrakt aus HeLa-Zellen in Gegenwart von [γ32]-ATP inkubiert. In diesem Ansatz konnten nur die Peptide phosphoryliert werden, welche die A.s. Thr-27 und Ser-35 umgebenden PKC-Motive besitzen. Während das Peptid PB-(16-35), das nur die Phosphoaminosäure Thr-27 in zentraler Position enthält, schwach phosphoryliert wurde, zeigten sich für die Fragmente PB-(21-40) und PB-(26-45) deutlichere Signale, was bereits als ein Hinweis für die entscheidende Rolle der Phosphoaminosäure Ser-35 gewertet werden kann. Abb. 5.3.4 Bestimmung der PB1-F2 Phosphorylierungsstellen durch überlappende Peptide. Die PB1-F2-Sequenz-überlappende 20mer-Peptide wurden in vitro mit HeLa-S10-Extrakt inkubiert, in einem 15%igen SDS-Gel aufgetrennt und mittels Autoradiographie analysiert. Nur die Peptide PB21-40 und PB26-45 wurden effizient durch zelluläre Kinasen phosphoryliert. Dasselbe PhosphorylierungsMuster ergab sich, wenn das Experiment mit der PKC aus Rattenhirn wiederholt wurde (Abbildung unterhalb). Das Experiment wurde anschließend unter Verwendung der aufgereinigten, kommerziellen PKC wiederholt. Wie bereits für den S10-Extrakt gezeigt, konnten vor allem die Peptide, welche ein zentral lokalisiertes Serin in Position 35 aufweisen effizient phosphoryliert werden (Abb. 5.3.4, Unterhalb). Um genauer festlegen zu können, welche der beiden A.s. Thr-27 bzw. Ser-35 effizient phosphoryliert werden, wurde das Peptid PB-(21-40) in vitro mit aufgereinigter PKC phosphoryliert und massenspektrometrisch untersucht. Nach einer ESI51 Ergebnisse MS-Analyse konnte nur eine Monophosphorylierung des Peptidfragmentes für das Serin in Position 35 detektiert werden. Eine Analyse des Gesamtlängen-Proteins nach S10-ExtraktPhosphorylierung war aus methodischen Gründen nicht möglich (Daten nicht gezeigt). 5.3.5 Mutationsanalysen zur Identifikation der relevanten Phosphorylierungsstellen von PB1-F2 in vivo Um die zentrale Rolle von Ser-35 für die PB1-F2-Phosphorylierung näher zu bestimmen, wurde eine mutierte sPB1-F2-Variante mit einem Aminosäureaustausch von Ser-35 zu Asn35 (S35N) unter den gleichen Bedingungen wie das synthetische Wildtyp-Protein mit HeLaS10-Extrakt in vitro phosphoryliert (Abb. 5.3.5A). Obwohl dieser Aminosäureaustausch in einer dramatischen Reduktion der PB1-F2-Phosphorylierung resultierte, konnte noch ein Restsignal detektiert werden, was auf die Präsenz einer weiteren Phosphorylierungsstelle schließen lässt. Diese Beobachtung steht im Einklang mit dem Phosphorylierungsmuster der überlappenden Peptidfragmente, welches bereits oberhalb gezeigt wurde (Abb. 5.3.4). In einem weiteren Experiment wurden 293T-Zellen mit CMV-Promotor-regulierten Expressionsplasmiden transient transfiziert, welche entweder für Wildtyp-PB1-F2 oder für entsprechende Mutanten des Proteins mit Aminosäure-Austauschmutationen innerhalb der Phopshorylierungsstellen Thr-27 (T27N), Ser-35 (S35N), Ser-84 (S84N) oder eine Doppelmutation (T27S35N) exprimieren. Die Zellen wurden mit [32P] radioaktiv markiert und die verschiedenen PB1-F2-Varianten immunopräzipitiert, auf einem SDS-Proteingel aufgetrennt und mittels Autoradiographie detektiert (Abb. 5.3.5B). Gleichzeitig wurden Proben der so isolierten Proteine im Westernblotverfahren analysiert, um eventuelle Schwankungen der Proteinmengen zwischen den verschiedenen Ansätzen detektieren zu können (siehe unterhalb). In Relation zur jeweils im Westernblot observierten Proteinmenge, konnte für die Mutanten PB1-F2-S84N oder PB1-F2-T27N kein Einfluss auf die Proteinphosphorylierung festgestellt werden, wohingegen die PB1-F2-S35N-Mutante einen deutlichen Signalverlust aufweist. Des Weiteren führte die Mutation von beiden Phosphorylierungsstellen in Position Thr-27 und Ser-35 zum völligen Verlust des radioaktiven Signals, wodurch Thr-27 eindeutig als alternative Phosphorylierungsstelle identifiziert und Ser-84 ausgeschlossen werden konnte. Abschließend wurde getestet, ob die identifizierten Phosphorylierungsstellen auch für virales PB1-F2 von Bedeutung sind. Hierfür wurden MDCK-Zellen mit dem IAVPR8-Stamm infiziert, der das Wildtpy-PB1-F2 exprimiert, oder mit einem rekombinanten Virus, welches ein 27 mutiertes 35 Aminosäureaustausch in Position Thr-27 und Ser-35 besitzt (T I/S L). 52 PB1-F2 mit Ergebnisse Abb. 5.3.5 Mutationsanalysen zur Identifizierung der PB1-F2 Phosphorylierungsstellen. (A) Das sPB1-F2-Protein mit einer Aminosäure-Austauschmutation von Serin 35 zu Asparagin (S35N) wurde in vitro mit S10-Extrakt aus HeLa-Zellen inkubiert und mittels Autoradiogrpahie des 15%igen SDS Gels analysiert. Die MOCK-Kontrolle verdeutlicht, dass kein Hintergrundsignal vorhanden war. (B) Transfektion von 293T-Zellen mit entweder dem pCMV-PB1-F2-Wildtyp-Expressionsvektor oder Mutanten, welche Aminosäure-Austauschmutationen in Position 27, 35 und 84 besitzen oder einer Doppelmutante für die Positionen 27 und 35. Die Westernblot-Kontrolle unterhalb zeigt die Proteinmenge der IP in Relation zum Phosphorylierungssignal an. (C) Radioaktive 32P-Markierung von MDCK-Zellen, welche mit IAVPR8-Wildtyp-Virus oder der IAVPR8-Mutante T27I/S35L infiziert und 8 h inkubiert wurden. Die Virusprotein-Menge in den Zelllysaten wurde im Westernblot detektiert. PB1-F2 wurde durch einen spezifischen Antikörper immunopräzipitiert und mittels Autoradiographie detektiert. Die Austauschmutationen wurden so gewählt, dass es zu keinen Änderungen im Leserahmen des pb1-Gens der viralen Polymerase kommen konnte. Die Westernblot-Kontrolle erfolgte mit Antikörpern, die spezifisch für das virale Nukleoprotein und zelluläres β-Actin sind, um detektieren zu können, ob die Infektion tatsächlich erfolgt ist und vergleichbare Mengen an IAV Protein für das Wildtyp-Virus als auch das mutierte Virus vorhanden sind (Abb. 5.3.5C). Während in Wildtyp-IAVPR8 infizierten Zellen phosphoryliertes PB1-F2 deutlich detektiert werden kann, zeigte sich im Ansatz mit der Doppelmutante kein Signal, obwohl in beiden Ansätzen wie in der Westernblot-Kontrolle zu sehen ist, vergleichbare Mengen virales PB1F2 im Zelllysat vorhanden waren. Dieser Befund steht im Einklang mit den zuvor in vitro erstellten Daten und unterstreicht die zentrale Bedeutung der PKC-Phosphorylierungsstellen Thr-27 und Ser-35 für PB1-F2 im Kontext IAV infizierter Zellen. 53 Ergebnisse 5.3.6 Die PB1-F2-Phosphorylierungsstelle Serin-35 ist in zahlreichen humanpathogenen Isolaten konserviert Nachdem die PB1-F2-Phosphorylierungsstellen identifiziert waren, sollte geklärt werden, ob diese auch in den Sequenzen anderer humanpathogener Virusisolate zu finden sind, was eine Voraussetzung für eine generelle biologische Funktion der Phosphorylierung von PB1-F2 wäre. Hierfür wurden 2324 Sequenzen von verschiedenen Isolaten verglichen, die entweder für das komplette PB1-F2-Protein oder eine verkürzte, ebenfalls häufig auftretende Variante kodieren (Tab. 2). Es zeigte sich, dass das Serin in Position 35 in den meisten Isolaten annähernd zu 100% konserviert ist, besonders in dem aktuell zirkulierenden H3N2-Isolat, das in dieser Analyse mit annähernd 50% aller bekannten Sequenzen vertreten ist, wohingegen Thr-27 in den H1N1- bzw. H3N2-Isolaten kaum vertreten ist. Auffälligerweise ist in den wenigen Isolaten, die kein Serin in Position 35 besitzen, das Thr-27 zu 100% konserviert, was ein Hinweis darauf sein könnte, dass Thr-27 als alternvative Phosphorylierungsstelle dient. IAV Isolat H1N1* 90/87A.s. 57A.s. H1N2 90A.s. H2N2 90A.s. H3N2** 90A.s. H5N1*** 90A.s. H9N2***90/92A.s. Anzahl der Sequenzen 20 343 25 29 1435 102 6 Konservierung von Thr-27 [%] 85 17,5 0 100 25,7 100 100 Konservierung von Ser-35 [%] 95 99,7 100 0 94,6 100 100 Tab. 2 Sequenzanalyse der PB1-F2 Phosphorylierungsstellen von humanen IAV Isolaten. Sequenzabgleich von 2324 Isolaten, welche für humane IAV-Infektionen relevant sind. Die Konservierung der identifizierten Phosphorylierungsstellen wurde unter Berücksichtigung der Proteinlänge und der Anzahl der vorhandenen Sequenzen bestimmt. *Die aktuell zirkulierenden Isolate exprimieren überwiegend ein C-terminal-verkürztes PB1-F2 mit einer Länge von 57 A.s., **7,2% der Sequenzen sind kürzer als 90 A.s., ***keine humanen Isolate, aber dennoch relevant, da direkte Infektionen von Menschen bekannt sind. Diese Analysen wurden zum Teil in Kooperation mit Dr. Viktor Wray und Hr. Karsten Bruns vom HZI in Braunschweig durchgeführt. 5.3.7 Die Mutation der PB1-F2-Phosphorylierungsstellen resultiert in einer reduzierten Caspase-3-Aktivierung in primären humanen Monozyten Um zu überprüfen, ob die Mutation der PKC-Phosphorylierungsstellen einen möglichen Einfluss auf die zuvor beschriebene und durch PB1-F2-verstärkte Apoptoseinduktion in monozytären Zellen hat (Chen, Calvo et al. 2001), wurden primäre humane Monozyten mit dem IAVPR8 Wildtyp-Virus, dem Phosphorylierungsstellen-Mutierten IAVPR8 (T27I/S35L) oder durch ein PB1-F2-defizientes Virus (PR82xΔF2) in einem Mehrfachansatz infiziert. Zuvor 54 Ergebnisse wurden die Titer der verschiedenen Virus-Stocklösungen mittels Plaque-Assay bestimmt und auf eine MOI von 1 normalisiert, um zu gewährleisten, dass alle Ansätze mit der gleichen Zahl an infektiösen Viruspartikeln infiziert wurden. Im Vergleich zu den MOCK-infizierten Kontrollzellen konnte in den infizierten Monozyten nach 20 h eine deutlich gesteigerte Aktivität der apoptotischen Effektorcaspase-3 gemessen werden. Während das Wildtyp-Virus die maximale Caspase-3-Aktivität induziert, war die Aktivität für das PB1-F2-(T27I/S35L)Phosphorylierungsstellen-mutierte Virus oder die (PR82xΔF2)-Mutante deutlich reduziert (Abb.5.3.7). Jeder Ansatz wurde achtfach wiederholt um mögliche Fehlerschwankungen innerhalb der Infektionen oder der Caspasen-Aktivitätsmessungen statistisch zu berücksichtigen. Im Gegensatz zu den bisher verwendeten Epithelzelllinien verläuft die Infektion und IAV-Replikation in Monozyten unproduktiv. Deshalb wurde der Ansatz mit denselben Stocklösungen und einer höheren MOI von 5 wiederholt, um die zelluläre Expression von Virusprotein (NP) nach der IAVPR8-Wildtyp-Infektion mit der Proteinmenge der mutierten Viren im Westernblot vergleichen zu können (Abb. 5.1.7B). A B Caspase 3-Aktivität [RLU] Caspase 3-Aktivierung in prim ären Monozyten für 20 h nach einer IAV(PR8) Infektion (MOI 1) 12000 10000 8000 6000 4000 2000 0 Kontrolle PR8-Wildtyp PR8PR8ΔPB1-F2 (27+35)PB1-F2 Abb. 5.3.7 Caspase-3-Aktivierung nach der Infektion von primären humanen Monozyten. (A) Primäre Monozyten wurden mit einer MOI von 1 mit dem PR8-Wildtyp-Virus, einer PB1-F2Virusmutante mit Aminosäureaustausch in Position Thr-27 und Ser-35 oder einer PB1-F2-deletierten Mutante infiziert und nach 20 h lysiert. Die Lysataktivität der apoptotischen Caspase-3 wurde über ein spezifisches Substrat mittels Lumineszenz gemessen. (B) Westernblot-Kontrolle infizierter Monozyten (MOI 5) nach 20 h. Die Expression an viralem Nukleoprotein (NP) ist zu diesem Zeitpunkt bei allen Virusvarianten vergleichbar. Die Zelllysate der verschiedenen Ansätze zeigten 20 h nach der Infektion eine quantitativ vergleichbare NP Expression, was belegt, dass die eingeführten Mutationen keinen signifikanten Einfluss auf die virale Proteinsynthese oder Replikation haben. Dieses Resultat 55 Ergebnisse kann als Indiz gewertet werden, dass die PKC-Phosphorylierungsstellen relevant sind für eine mögliche funktionelle Bedeutung in der PB1-F2-verstärkten Apoptose. Im Gegensatz hierzu gibt es Befunde, dass die Mutation der PB1-F2-Phosphorylierungsstellen keinen Einfluß auf die Apoptoseinduktion in MDCK-Zellen hat und auch die IAV-Replikation in diesen Zellen nur geringfügig und zeitabhängig beeinträchtigt wird (Daten nicht gezeigt). 5.4 Biochemische Charakterisierung der Oligomerisierung des PB1-F2-Proteins In vorangegangenen Arbeiten unseres Labors konnte mit einem spezifischen Antikörper gegen PB1-F2 im Westernblot gezeigt werden, dass sowohl sPB1-F2 als auch virales PB1-F2 selbst unter denaturierenden Bedingungen nach der Auftrennung im Standard-SDS-Gel in der Lage ist, Dimere auszubilden (Henklein, Bruns et al. 2005). Des Weiteren ist bekannt, dass PB1-F2 mit biologischen Membranen interagiert und zu deren Destabilisierung beiträgt (Chanturiya, Basanez et al. 2004), was für membraninteragierende, oligomerisierende Proteine charakteristisch ist und möglicherweise zur pro-apoptotischen Funktion des Proteins beiträgt (Zamarin, Garcia-Sastre et al. 2005). 5.4.1 Das PB1-F2-Protein zeigt eine deutliche Tendenz zur Ausbildung von Oligomeren Um das Oligomerisierungsphänomen genauer charakterisieren zu können, wurden molekular quervernetzende Substanzen, sogenannte chemische Crosslinker verwendet, welche im Falle einer Protein-Protein-Interaktion eine kovalente Bindung ausbilden, die auch unter den denaturierenden Bedingungen eines SDS-Gels erhalten bleibt. Die hier verwendeten chemischen Crosslinker geben bis zu einem 101fachen molaren Überschuss zum jeweiligen Protein eine spezifische Indikation für eine Interaktion mit potentiellen molekularen Bindungspartnern (Herstellerangaben). Die Behandlung von sPB1-F2 mit einer Variation an Crosslinkern resultierte in der Ausbildung von hochmolekularen, deutlich definierten Multimeren des Proteins bis hin zum Pentamer, welche im Westernblot detektiert werden konnten (Abb.5.4.1). Alle hier verwendeten Crosslinker, „bis(sulfosuccinimidyl)suberate“ (BS3), „ethylene glycol disuccinate di(N-succinimidyl)ester“ (EGS), „glutaraldehyde“ (GA) und „disuccinimidyl suberate“ (DSS) generierten ein spezifisches Oligomerisierungsmuster, welches auch im Crosslinker-Unterschuss (e-g) in der Ausbildung von dimeren (EGS, GA) oder trimeren (BS3, DSS) Formen des sPB1-F2-Proteins resultierte. Interessanterweise zeigte sich bei allen Crosslinker-Spezies im 103fachen Überschuss fast kein oder ein nur abgeschwächtes Bandenmuster (Reihe a), was darauf zurück zu führen ist, dass sich bei extremer Quervernetzung hochmolekulare Komplexe bilden, die im SDS-Gel nicht mehr 56 Ergebnisse aufgetrennt werden können, woraus eine reduzierte Signalintensität der verbleibenden Multimere resultiert (Bruns, Studtrucker et al. 2007). Abb. 5.4.1 Oligomerisierung von PB1-F2 in Abhängigkeit von verschiedenen chemischen Crosslinkern. Jeweils 100 ng sPB1-F2 wurde mit verschiedenen Molaritäten der chemischen Crosslinker BS3, EGS, GA und DSS im Bereich von 103 bis10-3 (a-g) inkubiert, mittels 12%igem SDS-Gel aufgetrennt und im Westernblot mit einem serumspezifischen Antikörper analysiert. 5.4.2 Das N-terminale PB-(1-40)- und C-terminale PB-(50-87)-Fragment von PB1-F2 besitzt die inhärente Fähigkeit zu oligomerisieren Das PB1-F2-Protein kann in einen unstrukturierten N-terminalen Teil und eine strukturierte, α-helikale Region, die sich im C-Terminus von A.s. Ile-55 bis Lys-85 erstreckt, unterteilt werden (Bruns, Studtrucker et al. 2007). Um eingrenzen zu können, welche der beiden Regionen des Proteins für das Oligomerisierungsphänomen relevant ist, wurden für weitere Untersuchungen Peptide verwendet, die entweder die ersten 40 A.s. (PB-(1-40)) oder den Cterminalen und strukturierten Bereich (PB-(50-87)) von PB1-F2 umfassen. Es zeigte sich, dass das PB-(50-87)-Fragment das größere Potential zur Ausbildung von Oligomeren im Vergleich zu PB-(1-40) besitzt (Abb. 5.3.2.1). PB-(50-87) war bereits in einem 10fach molaren DSS-Überschuss in der Lage, Dimere auszubilden, wohingegen PB-(1-40) erst ab einem 100fachen, unspezifischen DSS-Überschuss Multimere generiert (Abb. 5.4.2.1A). Die Tendenz des Fragmentes PB-(50-87) zu dimerisieren (Sternmarkierung), war deutlich 57 Ergebnisse ausgeprägter als bei dem N-terminalen Fragment und bei vergleichbarer Intensität auch noch im DSS-Unterschuss zu sehen (Abb. 5.3.2.1A, unteres Feld). In einem weiteren Ansatz wurden bei gleichbleibendem 1-molaren DSS-Überschuss verschiedene Konzentrationen der Peptide von 100 ng bis 1 µg je Ansatz verwendet (Abb. 5.3.2.1B). A B Abb. 5.4.2.1 Oligomerisierungsmuster der N- und C-terminalen Fragmente von PB1-F2. (A) PB-(1-40) und PB-(50-87) wurden mit abnehmenden Konzentrationen DSS inkubiert, in einem 12%igen SDS-Gel separiert und im Westernblot mit einem Serumantikörper gegen sPB1-F2 detektiert. In allen Ansätzen (a-g) wurden 25 ng Peptid aufgetrennt, im Feld unterhalb der PB-(50-87)-Sektion wurden 50 ng Peptid verwendet. (B) 0,1-1 µg der Fragmente PB-(1-40) bzw. PB-(50-87) wurde mit einem 1molaren Überschuss-DSS inkubiert, mittels 12%igem SDS Gel aufgetrennt und im Westernblot analysiert. Es zeigte sich, dass 400 ng des N-terminalen Fragmentes nötig waren um dasselbe Oligomerisierungsmuster zu erhalten, wie für 100 ng PB-(50-87). Die Analyse eines Fragmentes, das den mittleren Bereich des Proteins repräsentiert (PB-(30-70)), zeigte, dass dieses zwar in der Lage ist, über das einzige Cystein des Proteins in Position 42 Dimere auszubilden, aber im Vergleich zu den zuvor untersuchten Fragmenten PB-(1-40) und PB(50-87) keine Multimere aufweist (Daten nicht gezeigt). In einem weiteren Experiment sollte untersucht werden, ob und bis zu welcher Intensität die zuvor beschriebenen N- und Cterminalen Peptidfragmente mit PB1-F2 interagieren können. Hierfür wurden je Ansatz 100 ng sPB1-F2 mit einer äquimolaren Menge an DSS und steigenden Konzentrationen der 58 Ergebnisse jeweiligen Fragmente inkubiert (Abb. 5.4.2.2A+B). Die Intensität der heterogenen Bandenmuster nimmt in Abhängigkeit der steigenden Fragmentkonzentrationen zu, wobei das Peptid PB-(50-87) bereits ab 200 ng die maximale Ausbildung von Heterooligomeren aufweist (Abb. 5.4.2.2B) und PB-(1-40) die 2,5fache Menge bis zum Intensitätsmaximum benötigt (Abb. 5.4.2.2A). A B Abb. 5.4.2.2 Fragmentinkubation von sPB1-F2 und Ausbildung von Heterooligomeren. Zu jeweils 100 ng sPB1-F2 wurden steigende Konzentrationen von PB-(1-40) (A) und PB-(50-87) (B) zugegeben, mit einer zu sPB1-F2 äquimolaren Menge DSS inkubiert und im Westernblot-Verfahren analysiert. Die Heterooligomere sind mit einem Pfeil, die PB1-F2-Oligomere mit einem Stern markiert. Aus diesen Resultaten kann geschlussfolgert werden, dass sowohl das N-terminale als auch das C-terminale Fragment zur Multimerisierung tendieren, wobei das Letztere ein höheres Oligomerisierungspotential besitzt. Die Ergebnisse stimmen mit in silico Daten überein, welche für den C-Terminus zwei potentielle Oligomerisierungsmotive für A.s. 54-58 und A.s. 68-72 und ein schwächeres Motiv für den N-Terminus mit A.s. 9-13 vorausgesagt hatten (Bruns, Studtrucker et al. 2007). 59 Ergebnisse 5.4.3 Das Cystein in Position 42 ist durch die Ausbildung von Disulfidbrücken an der Oligomerisierung von PB1-F2 beteiligt Das PB1-F2-Protein besitzt nur ein einziges Cystein in Position 42 welches in der Lage wäre, über seine Sulfhydryl-Gruppe eine Disulfidbindung einzugehen, um zur Selbstassoziation von PB1-F2 beizutragen. Um den Einfluss dieses Phänomens auf die PB1-F2-Oligomerisierung analysieren zu können, wurde das Protein in Gegenwart des chemischen Reduktionsmittels DTT (1 mM) inkubiert und anschließend einer Crosslinker-Reaktion unterzogen (Abb. 5.4.3A). Dieser Ansatz zeigte annähernd dasselbe Oligomerisierungsmuster wie ein paralleler Kontrollansatz ohne DTT. Die Ausbildung von trimeren und tetrameren Banden war jedoch unter den stark reduzierenden Bedingungen weniger effizient. In einem weiteren Kontrollansatz wurde das Experiment mit der 100fachen Menge an sPB1-F2 im Vergleich zum vorangegangenen Ansatz wiederholt um die Detektion der Oligomere mittels Coomassiefärbung zu ermöglichen und somit eine zum antikörperbasierten Westernblot alternative Analyse vornehmen zu können. Die Ansätze wurden mit 2- oder 20fachem molaren DSS-Überschuss in Gegenwart von β-Mercaptoethanol (βME) oder ohne das Reduktionsmittel inkubiert. Bereits bei einem 2-molaren DSS-Überschuss zeigte sich das maximal detektierbare Oligomerisierungsmuster, welches mit dem in der sensitiveren Westernblot-Methode übereinstimmt, was belegt, dass alle oligomere Strukturen mit dem Serumantikörper detektiert werden können (Abb. 5.4.3B). A B Abb. 5.4.3 Analyse der PB1-F2 Oligomersierung unter reduzierenden Bedingungen. (A) Jeweils 100 ng sPB1-F2 wurden mit einem 2fachen molaren Überschuss an DTT inkubiert und anschließend einer Crosslink-Reaktion mit äquimolaren Mengen DSS unterzogen. Die Auftrennung der Oligomere erfolgte in einem 12%igen SDS-Gel mit anschließender Detektion durch einen PB1-F2spezifischen Antikörper im Westernblot. (B) 2,5 µg sPB1-F2 wurden mit einem 2- oder 20fachen Überschuss an DSS inkubiert und in einem 15%igen SDS-Gel unter reduzierenden (ßME) oder nicht reduzierenden Bedingungen aufgetrennt um mit Coomassie-Blau gefärbt. 60 Ergebnisse Die hochmolekularen Aggregate im 20fach molaren DSS-Überschuss konnten in diesem Gelsystem nicht mehr aufgetrennt werden, woraus das abgeschwächte Signal für diesen Ansatz resultiert. Des Weiteren zeigte sich ein deutlicher Einfluss des Reduktionsmittels βME auf die Ausbildung von PB1-F2-Dimeren. Im Vergleich zum Standardansatz wurde die dimerisierende Eigenschaft des Proteins in Gegenwart von βME annähernd neutralisiert, wohingegen die Ausbildung von Multimeren nicht signifikant beeinträchtigt wurde. Zusammenfassend wurde gezeigt, dass das Oligomerisierungsphänomen von PB1-F2 sowohl auf sequenzspezifische Interaktion als auch auf die Ausbildung von Disulfidbindungen zurückzuführen ist und mit dem C- oder N-terminalen Fragment in Gegenwart von sPB1-F2 Heterooligomere ausgebildet wurden, welche die inhärente Fähigkeit des Proteins zur Selbstaggregation zusätzlich belegen. 61 Diskussion 6 Diskussion 6.1 PB1-F2, ein viraler Pathogenitätsfaktor und die Frage nach den molekularen Mechanismen Es sind bereits sieben Jahre vergangen seit in einem Screening nach MHC-I-Epitopen, die sich nach einer IAVPR8-Infektion von viralen Polypeptiden ableiten lassen, welche außerhalb des Standard-Leserahmens exprimiert werden, ein neuartiges Influenza-Protein mit der Bezeichnung PB1-F2 entdeckt wurde. Seit dieser Zeit wurden zahlreiche Anstrengungen unternommen, die molekularen Mechanismen der PB1-F2-vermittelten Funktionen zu klären. Da zunächst beobachtet wurde, dass PB1-F2 eine mitochondriale Lokalisationssequenz (MTS) besitzt und in den Mitochondrien von transfizierten und infizierten Zellen lokalisiert ist, wurde angenommen, dass es sich um ein Regulatorprotein der virusinduzierten, intrinsischen Apoptose handelt, welches pro-apoptotische Eigenschaften besitzt (Chen, Calvo et al. 2001; Gibbs, Malide et al. 2003; Yamada, Chounan et al. 2004). Tatsächlich konnte in Pull-down-Experimenten gezeigt werden, dass PB1-F2 mit den Untereinheiten des mitochondrialen PTPC interagiert (Zamarin, Garcia-Sastre et al. 2005). Scheinbar konträr zu diesen Befunden wurde berichtet, dass apoptoseverstärkende oder-inhibierende Effekte durch PB1-F2 in den IAV-relevanten Epithelzelllinien MDCK, MDBK und A549, nach einer Infektion von PB1-F2-defizientem Virus, im Vergleich zum Wildtyp-Virus nicht detektiert werden konnten (Chen, Calvo et al. 2001). Dies war bereits ein erster Hinweis, dass die proapoptotischen Effekte des Proteins entweder zellspezifisch oder möglicherweise in Zellkultur nicht relevant sind. Mitochondrienspezifische Apoptosemarker, welche direkt durch intrazelluläres PB1-F2 aktiviert wurden, wie z.B. die Freisetzung von Cytochrom-c, konnten bisher nur in vitro beobachtet werden. Nach der Transfektion von 293T-Zellen wurde ein apoptoseverstärkender Effekt von PB1-F2 mittels PARP-Spaltung im Westernblot detektiert, aber nur dann, wenn die Zellen vorher mit apoptotischen Stimuli zusätzlich sensibilisiert wurden (Zamarin, Garcia-Sastre et al. 2005). Tatsächlich konnte bisher allein durch die Präsenz von PB1-F2 in Zellkultur keine Apoptoseinduktion nachgewiesen werden, die zur Generierung der typischen morphologischen Merkmale oder einem deutlich messbaren Zelltod geführt hätte. Dementsprechend sind die molekularen Mechanismen einer möglichen intrinsischen Apoptoseinduktion noch vollkommen ungeklärt. Weiterhin zeigte PB1-F2 nach der Infektion mit dem PR8- oder WSN-Isolat keinerlei Einfluss auf die IAV-Replikation in Zellkultur oder in der Maus (Zamarin, Ortigoza et al. 2006). Durch ein attenuiertes, mauspathogenes Virus und einer PB1-F2-depletierten Mutante hiervon 62 Diskussion konnte gezeigt werden, dass einige Tage nach der Infektion mit dem PB1-F2 defizienten Virus deutlich weniger Viruspartikel in den Lungen der infizierten Tiere nachweisbar waren, was auf eine mögliche immunmodulatorische Funktion von PB1-F2 rückschließen lässt. Dafür spricht auch der Befund, dass der Virustiter-peak in den Lungen infizierter Mäuse, die mit einem mutierten PR8-Virus infiziert wurden, welches das PB1-F2-Protein der Spanischen Grippe exprimiert, schneller erreicht wurde als mit dem Wildtyp-PR8-Isolat, aber für beide Viren zu keinem Zeitpunkt eine höhere Viurslast gemessen werden konnte (McAuley, Hornung et al. 2007). Dass PB1-F2 für die IAV-Replikation nicht essentiell ist, scheint schlüssig, da das Protein nicht in allen Isolaten präsent ist und auch nicht hinreichend geklärt ist, ob die Expression in den PB1-F2-kodierenden Isolaten auch tatsächlich und vergleichbar erfolgt. Es wird angenommen, dass PB1-F2 möglicherweise für die zellspezifische Zerstörung alveolarer Makrophagen relevant sein könnte, da ein apoptoseverstärkender Effekt im Kontext einer Virusinfektion bisher nur in einer monozytären Zelllinie gezeigt werden konnte (Chen, Calvo et al. 2001; Lowy 2003). Molekulare Mechanismen, welche diese Hypothese stützen, sowie eine mögliche pro-apoptotische Bedeutung von PB1-F2 im Kontext der Depletion von Immunzellen, wie sie oftmals bei schwerwiegenden Influenza-Infektionen im Menschen zu beobachten ist (Criswell, Couch et al. 1979), wurden bisher noch nicht experimentell erbracht. Neuere Daten bestätigten die Rolle von PB1-F2 als viralen Pathogenitätsfaktor (Conenello, Zamarin et al. 2007; McAuley, Hornung et al. 2007). Im Mausmodell wurde gezeigt, dass eine singuläre A.s.-Austauschmutation im C-Terminus von PB1-F2 in Position 66 ausreichend war, um ein IAV-Isolat von moderater Pathogenität in ein hochpathogenes zu konvertieren. Für dieses Phänomen konnte jedoch bisher keine funktionelle Erklärung erbracht werden. Ebenso interessante Daten lieferten die Insertionen von A.s.-Austauschmutationen in die Sequenz eines vom IAVPR8-Isolat exprimierten PB1-F2-Proteins, das auf diese Weise an ein PB1-F2-Protein aus einem Isolat der Spanischen Grippe adaptiert wurde. Das so veränderte Virus zeigte neben gesteigerter Virulenz und Plaquegröße in Zellkultur auch dramatische Effekte auf die Zerstörung des Lungengewebes von Mäusen im Kontext einer bakteriellen Koinfektion, was zusammen mit einer erhöten Zytokin- und Chemokindetektion in der Lungenlavage der Tiere beschrieben wurde (McAuley, Hornung et al. 2007). Trotz der eindeutig sequenzspezifischen pathogenen Wirkung, die sich für virales PB1-F2 im Tiermodell zeigt, ist es auch hierfür bisher nicht gelungen, die molekularen Mechanismen, die für diese Effekte verantwortlich sind, zu klären. Es wurde auch diskutiert, dass die pathogenen Effekte möglicherweise vollkommen unabhängig von der pro-apoptotischen 63 Diskussion Funktion des Proteins zu betrachten sind, da keine Verbindung zum induzierten Zelltod und dem zerstörten Lungengewebe der Versuchstierere hergestellt werden konnte, sondern vielmehr als nekrotische Auswirkungen der Inflammation beschrieben wurden (McAuley, Hornung et al. 2007). Nach neuesten Erkenntnissen interagiert PB1-F2 mit der viralen PB1Polymerase (Mazur, Anhlan et al. 2008). Der knock out von PB1-F2 resultierte in einer reduzierten Polymeraseaktivität und einer kleineren Plaque-Morphologie, zeigte aber keinerelei Unterschiede im Replikationsverhalten im Vergleich zum Wildtyp-Virus. Es könnte sich hier wie im Falle der PB1-F2-induzierten Apoptose ebenfalls um einen Effekt handeln, der in Zellkultur nur schwer zu detektieren ist, da MDCK-Zellen bezüglich der Virusreplikation optimiert sind (Mazur, Anhlan et al. 2008). Die Infektion mit einer PB1-F2defizienten Mutante resultierte in der verfrühten Translokation des PB1-Proteins in das Zytoplasma der infizierten Zelle. In diesem Zusammenhang wird spekuliert, dass PB1-F2 durch die gezielte Interaktion mit PB1, dessen Retention im Nukleus steuert, was wiederum für eine effiziente RNA-Replikation von Bedeutung sein könnte. Es zeichnet sich zusehends ab, dass PB1-F2 ganz ähnlich wie die akzessorischen Proteine Vpr (HIV) oder p13 (HTLV) multifunktionell ist. Die Problematik, eindeutige Effekte des Proteins in Zellkultur zu ermitteln, gestaltet eine funktionelle Aufklärung der molekularen Mechanismen sehr schwierig und ist eine große aber auch notwendige Herausforderung für weitere Untersuchungen der PB1-F2-vermittelten Pathogenität. 6.2 Die Expression von PB1-F2 ist zeitlich reguliert Wie in dieser Arbeit gezeigt werden konnte, wurde PB1-F2 nicht nur in Eptihel-Zelllinien, sondern auch in CD4+-T-Zellen und primären Monozyten exprimiert. Bereits 4 h nach der Infektion kann virales PB1-F2 im Westernblot detektiert werden, was zunächst in Korrelation zu der jeweiligen Menge an neusynthetisiertem PB1 zu stehen scheint, welches zu den früh exprimierten IAV-Genprodukten gezählt wird. Die maximale PB1-F2-Expression ist 6-8 h nach einer Infektion erreicht, was im Einklang mit den zuvor beschriebenen Expressionsstudien in infizierten MDBK-Zellen steht (Chen, Calvo et al. 2001). Nach etwa 12 h nimmt die PB1-F2-Expression dramatisch ab (Daten nicht gezeigt) und kann nach 24 h nicht mehr detektiert werden, obwohl sich die PB1-Synthese kontinuierlich fortsetzt. Dieses Phänomen scheint einem generellen Mechanismus zu unterliegen, da es sowohl in primären Zellen (Monozyten) als auch allen hier untersuchten Zelllinien auftritt, wobei die molekulare Ursache dieser zeitlich regulierten PB1-F2-Expression gänzlich unbekannt ist. Es kann daher geschlussfolgert werden, dass die Expression von viralem PB1-F2 über mehr Mechanismen 64 Diskussion reguliert wird als die ursprünglich beschriebene Initiation eines sekundären Start-Codons (Chen, Calvo et al. 2001). In dieser Arbeit wurde gezeigt, dass die Transfektion eines PB1 Expressions- Plasmids in 293T-Zellen ausreichend ist, um eine kontinuierliche PB1-F2Expression zu induzieren, die auch noch nach 24 h nachgewiesen werden kann. Dies ist ein deutlicher Beleg dafür, dass die PB1-F2-Expression nach einer Infektion entweder durch virale Faktoren oder zelluläre Faktoren, welche im Kontext der Infektion reguliert werden, gesteuert wird. Bisher konnte nur das virale PB1-Protein bzw. die Komponenten des mitochondrialen VDAC (Voltage Dependent Anion Channel) als Bindungspartner von PB1F2 identifiziert werden (Zamarin, Garcia-Sastre et al. 2005; Mazur, Anhlan et al. 2008). Die PB1-PB1-F2-Interaktion wurde jedoch noch nicht in einen Zusammenhang mit der zeitlich regulierten Expression von PB1-F2 gebracht. Dass es sich jedoch um eine posttranslationale Regulation handelt, scheint sehr wahrscheinlich, denn PB1-F2 und PB1 teilen sich die gleiche mRNA, so dass eine spezifische Herunterregulation der RNA-Synthese auch in einer deutlich reduzierten PB1-Expression resultieren müsste. Weiterhin wurde gezeigt, dass die zeitlich regulierte PB1-F2-Expression durch Proteasominhibitoren verlängert werden konnte (Chen, Calvo et al. 2001). Ob und wie ein gezielter Abbau im Kontext der proteasomalen Degradierung erfolgt und welche Faktoren dafür verantwortlich sind, bleibt noch Gegenstand späterer Untersuchungen. 6.3 Exogenes sPB1-F2 zeigt keine zytotoxischen Effekte in Zellkultur Nach ursprünglichen Angaben ist die Präsenz von 50 nM sPB1-F2 im Zellkulturmedium ausreichend, um bereits nach 4 h zytotoxische Effekte zu induzieren (Chen, Calvo et al. 2001). Dies könnte auf zwei grundsätzlich unterschiedlichen Wegen geschehen. Zum einen wäre es denkbar, dass exogenes PB1-F2 durch den Kontakt mit einem Zellmembran-Rezeptor Signalkaskaden induziert, die letztlich den Zelltod herbeiführen. Andererseits besteht die Möglichkeit, dass PB1-F2, ähnlich dem Vpr-Protein von HIV, als trojanisches Peptid die Zellmembran durchdringt und direkt in den Mitochondrien apoptotische Prozesse in Gang setzt. Dafür würden auch die membrandestabilisierenden Eigenschaften des synthetischen Proteins sprechen, die zu einer transienten Porenbildung in der inneren und äußeren Mitochondrienmembran führen können (Chanturiya, Basanez et al. 2004; Zamarin, GarciaSastre et al. 2005). Ebenso wäre es denkbar, dass die Aufnahme von sPB1-F2 rezeptorvermittelt ist. Noch 5 h nach der Inkubation von HeLa-Zellen mit 300 nM sPB1-F2 konnte das Protein in gewaschenen und lysierten Zellen nachgewiesen werden. Auch dimere Spezies von PB1-F2 wurden im Westernblot detektiert, was zusätzlich für die Funktionalität 65 Diskussion des synthetischen Proteins spricht, welches die gleichen biochemischen Eigenschaften wie das virale PB1-F2 aufweist (Henklein, Bruns et al. 2005; Bruns, Studtrucker et al. 2007). Sogar 25 h nach der Inkubation waren noch Spuren von zellulärem sPB1-F2 zu sehen, was dafür spricht, dass das Protein ausreichend stabil ist, um eine mögliche exogene Funktion zu vermitteln. Dennoch konnte in einem Zeitraum von bis zu 50 h keine PB1-F2-vermittelte Apoptoseinduktion durch Annexinfärung oder zytotoxische Effekte durch parallele Propidiumiodid-Färbung gemessen werden. Im Gegensatz zu bereits publizierten Beobachtungen (Chen, Calvo et al. 2001) konnte im Rahmen dieser Arbeit auch nach extremer Erhöhung der sPB1-F2-Konzentration auf bis zu 10 µM oder durch eine Verlängerung der Inkubationszeit in verschiedenen Zelllinien keine Apoptose gemessen werden. Dabei war es überraschend festzustellen, dass sich neben der phosphatidylserinspezifischen Annexin-V-Färbung und der Caspase-3-Aktivierung auch kein Effekt auf die Änderung des mitochondrialen Potentiales messen ließ, selbst in der Präsenz von bis zu 10 µM sPB1-F2 und Kostimulation durch UV-Strahlung, was durch den Mitochondrien-sensitiven Farbstoff JC1 angezeigt wurde. Die Inkubation von Jurkat-Zellen mit sVpr, resultierte deutlich in der Generierung einer apoptotischen Zellpopulation, wie es bereits zuvor beschrieben wurde (Sherman, Schubert et al. 2002). Im Gegensatz zum chemischen Stimulus Etoposid, der in allen Zellen Apoptose induzierte, zeigte sich für sVpr ein zeitabhängiger Effekt, wobei in Korrelation zur Peptidstabilität die stärkste Induktion bereits nach 8 h Inkubationszeit gemessen wurde. Mit sPB1-F2 wurde zu keinem Zeitpunkt ein signifikanter Effekt detektiert. Daher bleibt es bis heute unklar und rein hypothetisch, ob exogenes PB1-F2 in vivo für eine pathogene Funktion wie z.B. der Depletion von Monozyten im Kontext einer IAV-Infektion im Lungengewebe verantwortlich ist (Chen, Calvo et al. 2001; Lowy 2003). Andererseits wurde durch intranasale Applikation von C-terminalem PB1-F2-Peptid in Mäusen das Lungengewebe der Tiere für eine bakterielle Überinfektion extrem sensibilisiert, was durch das N-terminate Kontrollpeptid nicht erfolgte (McAuley, Hornung et al. 2007). Der Befund, dass PB1-F2 alleine nicht in der Lage ist, in Zellkultur Apoptose zu induzieren, wurde durch später publizierte Daten bestätigt, welche aufzeigten, dass transfiziertes, Plasmid-exprimiertes PB1-F2 in Epithelzellen keine apoptotische Wirkung zeigt (Zamarin, Garcia-Sastre et al. 2005). Diese Daten wurden durch Aktivitätsmessungen der zellulären Effektorcaspase-3 in dieser Arbeit bestätigt und belegen, dass PB1-F2 auf den Kontext einer viralen Infektion oder zellulären Sensibilisierung angewiesen ist, um apoptotische Prozesse zu modulieren. Für endogen exprimiertes PB1-F2 konnte ein verstärkender Effekt auf die Apoptoseinduktion 66 Diskussion durch PARP-Spaltung in 293T-Zellen gezeigt werden, wenn diese Zellen zuvor mit apoptotischen Stimuli behandelt wurden (Zamarin, Garcia-Sastre et al. 2005). Die Sensibilisierung verschiedener Zelllinien unter Verwendung unterschiedlicher Stimuli und anschließende Inkubation mit sPB1-F2 resultierte in keiner verstärkten Apoptoseinduktion in Gegenwart des exogenen Proteins. Daher ist es fraglich, ob PB1-F2 überhaupt transduzierende Eigenschaften besitzt. Experimente, die eine exakte Unterscheidung zwischen Zellmembran-assoziiertem und tatsächlich internalisiertem Protein ermöglichen, lieferten bisher keine eindeutigen Ergebnisse. Des Weiteren besteht die Möglichkeit, dass endogenes PB1-F2 erst durch posttranslationale Modifikationen oder Protein-Interaktionen in einen funktionellen Zustand versetzt wird, der im Rahmen einer Inkubation mit dem exogenen, synthetischen Protein nicht gegeben ist. Die Modulation der virusinduzierten Apoptose ist vermutlich nur eine von zahlreichen Eigenschaften des akzessorischen PB1-F2-Proteins und scheint zellspezifisch zu sein. Im Kontext einer IAV Infektion der monozytären U937Zelllinie wurden nach Annexin-V-Färbung mehr apoptotische Zellen für ein PB1-F2exprimierendes Virus als für die entsprechende Knock-out-Mutante detektiert. In dieser Arbeit wurde ebenfalls eine gesteigerte Caspase-3-Aktivität nach der Infektion von PB1-F2exprimierendem Virus in primären, humanen Monozyten gemessen, was für einen deutlich zellspezifischen Effekt spricht. Im Gegensatz hierzu konnte kein Unterschied auf die Apoptoseinduktion nach der Infektion von MDCK-Zellen mit dem IAVPR8-Wildtyp-Virus und einem PB1-F2-deletierten PR8-Virus gemessen werden (Mazur, Anhlan et al. 2008). Daher scheint es wahrscheinlich, dass pro-apoptotische Funktionen des PB1-F2-Proteins eher im Kontext der Infektion von Immunzellen zu sehen sind (Lowy 2003), wobei die zentrale Funktion des Proteins in vivo vermutlich eher in der Regulation der Chemokin- und Zytokinantwort im Kontext einer bakteriellen Koinfektion liegt als in der Modulation der Apoptose und diese Effekte möglicherweise sogar getrennt zu sehen sind (McAuley, Hornung et al. 2007). 6.4 PB1-F2 ist ein Phosphoprotein und wird von der Proteinkinase C phosphoryliert Nach einer IAV-Infektion werden eine Vielzahl intrazellulärer Signalwege und Faktoren aktiviert, welche die zellulären Abwehrmechanismen regulieren oder den programmierten Zelltod induzieren (Ludwig, Pleschka et al. 2006). Um diese Prozesse zu steuern, stehen dem Influenza-A-Virus nur 11 bekannte Proteine zur Verfügung. Daraus folgt, dass die meisten Virusproteine multifunktionell sind und posttranslational modifiziert werden. In dieser Arbeit wurde gezeigt, dass PB1-F2 zu der wachsenden Liste der IAV-Phosphoproteine gehört 67 Diskussion (Privalsky and Penhoet 1981; Richardson and Akkina 1991; Arrese and Portela 1996; SanzEzquerro, Fernandez Santaren et al. 1998). Erste Hinweise hierfür ergaben sich durch die Beobachtung, dass PB1-F2 nach der Infektion von MDBK-Zellen in drei dicht nebeneinander migrierenden Proteinbanden mittels radioaktiver Markierung detektiert werden konnte (Chen, Calvo et al. 2001). Die In-silico-Vorhersage, dass PB1-F2 vier potentielle Phosphorylierungsstellen für die Proteinkinase C besitzt, steht dabei im Einklang mit der Tatsache, dass die PKC in der frühen Phase nach einer IAV-Infektion aktiviert wird (Arora and Gasse 1998; Root, Wills et al. 2000), also zu einem Zeitpunkt im Infektionsverlauf, der parallel mit der maximalen Expression von PB1-F2 korreliert. Weiterhin konnte gezeigt werden, dass der PKC-Inhibitor BIM den IAV-Eintritt in die Zelle dosisabhängig inhibieren konnte (Root, Wills et al. 2000). Dabei muss berücksichtigt werden, dass BIM ein potenter Inhibitor aller PKC Isoformen und im Besonderen für die konventionelle Subfamilie selektiv ist (Toullec, Pianetti et al. 1991). Die dominante Rolle der konventionellen PKC-Isoformen wurde inzwischen für frühe und späte Prozesse der IAV-Replikation beschrieben (Arora and Gasse 1998; Root, Wills et al. 2000; Marjuki, Alam et al. 2006). In Übereinstimmung hierzu konnte in einem Yeast Two Hybrid Screen die aktive PKCα als potentieller Bindungspartner von PB1-F2 ermittelt werden (nicht publizierte Daten). Daher ist eine direkte Interaktion von PB1-F2 mit der PKCα unmittelbar nach der Synthese der frühen Virusproteine sehr wahrscheinlich. Die für PB1-F2 identifizierten Phosphorylierungsstellen in Position 27 und 35 befinden sich in der zentralen, unstrukturierten Region des Proteins, für die im Gegensatz zum α-helikalen C-Terminus noch keine bekannte Funktion beschrieben ist. Die Lokalisation der Phosphorylierungsstellen im unstrukturierten Bereich von PB1-F2 stimmt mit früheren Untersuchungen überein, die potentielle Phosphorylierungsstellen in der unstrukturierten Region von Proteinen generell für wahrscheinlicher halten, da hierdurch die maximale Zugänglichkeit des aktiven Zentrums einer Kinase zum jeweiligen Erkennungsmotiv des Substratproteins gewährleistet ist (Roach 1991; Blom, Gammeltoft et al. 1999). Weiterhin wurde berichtet, dass sich besonders in den seit 1950 zirkulierenden H1N1-Isolaten zahlreiche C-terminal verkürzte 57 A.s.-Varianten des PB1-F2-Proteins befinden (Zell, Krumbholz et al. 2007), welche demnach weder über eine MTS noch eine Oligomerisierungsdomäne verfügen, aber immer noch beide potentielle Phosphorylierunsstellen besitzen, was im Rahmen der Sequenzanalysen in dieser Arbeit dargestellt wurde. Annähernd 100% der analysierten Sequenzen zeigten ein PKC-Motiv mit einem konservierten Serin in Position 35, wohingegen das Threonin in Position 27 nicht konserviert war und möglicherweise als alternative Phosphorylierungsstelle dient. Ob die Phosphorylierung von PB1-F2 für die publizierten pro68 Diskussion apoptotischen Effekte relevant ist (Chen, Calvo et al. 2001; Zamarin, Garcia-Sastre et al. 2005), kann jedoch aus den Sequenzanlaysen nicht geschlossen werden, da die volle Funktion von PB1-F2 möglicherweise erst durch die mitochondriale Lokalisation des phosphorylierten Proteins in seiner vollen Länge vermittelt wird. In MDCK-Zellen konnte nach einer Infektion mit dem IAVPR8-Laborstamm und einer entsprechenden Phosphorylierungsmutante hiervon mit Austauschmutationen in Position 27 und 35 kein Unterschied bezüglich der virusinduzierten PARP-Spaltung detektiert werden (nicht publizierte Daten). Im Gegensatz hierzu konnte die PB1-F2-vermittelte Apoptose durch die effizientere Aktivierung der apoptotischen Effektorcaspase-3 in primären Monozyten gemessen werden, was die zellspezifische Rolle dieses Phänomens erneut bestätigt und die Phosphorylierung von PB1F2 als möglicherweise funktionell relevant für die Apoptoseinduktion in Immunzellen erscheinen läßt. Dass die PB1-F2-Phopshorylierung auch intrazellulär mit der PKC im Zusammenhang steht, konnte nach der Applikation von PMA zu PB1-F2 transfizierten 293T Zellen gezeigt werden. Die Zugabe von PMA resultierte in einem verstärkten radioaktiven Phosphorylierungssignal im Vergleich zu nicht stimulierten Zellen. Dieses Ergebnis kann auf die Aktivierung der konventionellen PKC-Isoformen zurückgeführt werden, die erst durch Phorbolesterstimulation ihre volle Aktivität entfalten (Li and Gobe 2006). Komplementiert wurde der Befund durch die signifikante Inhibition der PB1-F2-Phosphorylierung in Gegenwart von Staurosporin, einem unspezifischen, aber potenten Inhibitor aller PKCIsoformen, sowie einem deutlich reduzierten Phsophorylierungssignal nach der Applikation von BIM. Für eine direkte Interaktion zwischen der PKC und PB1-F2 spricht auch die starke in-vitro-Phosphorylieung von PB1-F2 durch PKC-Extrakt aus Rattenhirn, welches sich überwiegend aus den konventionellen Isoformen zusammensetzt (Kikkawa, Go et al. 1986) und in der Lage war, sPB1-F2 vom PR8-Isolat und von einem Isolat der Spanischen Grippe zu phopshorylieren. Die zentrale Rolle der PKC konnte weiterhin durch die dosisabhängige Inhibition des durch S10-Extrakt phosphorylierten Proteins bestätigt werden, wohingegen der Kontrollinhibitor Wortmannin selbst in hohen Konzentrationen keinerlei Einfluss auf das Phosphorylierungssignal hatte. Die Kinasen der PKC-Familie sind in eine Vielzahl von Signalwegen und zellulären Funktionen involviert, wie z.B. der Proliferation, Differenzierung und Apoptose (Li and Gobe 2006). Im Gegensatz zur ursprünglichen Annahme, dass die Translokation der PKC zur Zytoplasmamembran eine Voraussetzung für deren Aktivierung und die darauf folgende Substratphosphorylierung ist, konnten die verschiedenen PKC-Isoformen in den unterschiedlichsten zellulären Kompartimenten gefunden werden, wie z.B. im Zytosol 69 Diskussion (Ahmad, Lee et al. 1984), am Zytoskelett (Nishikawa, Hidaka et al. 1983) und im Zellkern (Patskan and Baxter 1985). Nach einer Infektion ist PB1-F2 sowohl in den Mitochondrien als auch im Zytoplasma und im Nukleus der Zellen lokalisiert (Chen, Calvo et al. 2001). Die nukleäre Lokalisation des Proteins ist von mindestens einer viralen Komponente abhängig, da transfiziertes PB1-F2 ausschließlich in den Mitochondrien der Zellen zu finden ist. Dies schließt jedoch nicht aus, dass die Phosphorylierung von PB1-F2 möglicherweise für eine Funktion im Zellkern von Bedeutung ist. In einer anderen Arbeitsgruppe konnte gezeigt werden, dass die Mutation der Phosphorylierungsstellen in Position 27 und 35 in einem PB1F2-exprimierenden rekombinanten PR8-Virus in einer eingeschränkten Replikation in MDCK-Zellen zwischen 24 h und 36 h nach der Infektion resultiert (nicht publizierte Daten). Diese Beobachtung steht im Widerspruch zu bisherigen Publikationen, die für das PB1-F2Protein aus dem WSN- und PR8-Isolat keinen Einfluss auf die Replikation feststellen konnten (Zamarin, Ortigoza et al. 2006). Da PB1-F2 ein multifunktionelles Protein ist, kann davon ausgegangen werden, dass es sowohl replikationsfördernde, als auch beschränkende Funktionen besitzt. Im Falle der PB1-F2-defizienten Viren sind beide Eigenschaften möglicherweise aufgehoben, woraus kein messbarer Einfluss auf die Virusreplikation resultiert. Die PB1-F2-Phosphorylierung hat möglicherweise eine replikationfördernde Funktion, die in den Viren welche für die Phosphorylierungsstellen mutiert sind nicht mehr vorhanden ist, so dass replikationsbeschränkende Eigenschaften von PB1-F2 überwiegen. Die funktionelle Bedeutung der PB1-F2-Phosphorylierung durch die PKC bleibt noch Gegenstand weiterer Untersuchungen und könnte ein erster Schritt sein, um die in vivo vermittelte Pathogenität des Proteins auf molekularer Ebene zu klären. 6.5 PB1-F2 besitzt die intrinsische Eigenschaft, Oligomere auszubilden NMR-Analysen zeigten, dass PB1-F2 eine ausgeprägte Tendenz zur Selbstassoziation in wässriger Lösung besitzt und erst unter zunehmend hydrophoben Lösungsbedingungen αhelikale Abschnitte stabilisiert werden (Bruns, Studtrucker et al. 2007). Bisher ist es nicht gelungen, größere Mengen des rekombinanten Proteins herzustellen, wie es vor allem für Strukturanalysen nötig wäre. Zur Untersuchung des PB1-F2-Oligomerisierungsphänomens wurde das synthetische Protein benutzt, da es eine Reihe von Vorteilen für diese Studien aufweist. Zunächst kann es mit einer Länge von 87 A.s. mittels chemischer Festphasensynthese hergestellt werden (Henklein, Bruns et al. 2005), und störende Verunreinigungen, wie sie im Kontext einer klassischen Aufreinigung von rekombinantem Protein auftreten könnten, sind weitestgehend ausgeschlossen. Weiterhin zeigt das 70 Diskussion synthetische Protein die gleichen biochemischen Eigenschaften wie das virale PB1-F2 aus dem PR8-Isolat, einschließlich der Fähigkeit, selbst unter den denaturierenden Bedingungen eines SDS-Gels noch dimere und sogar trimere Strukturen auszubilden (Henklein, Bruns et al. 2005). Nach einer Mikroinjektion ist sPB1-F2 in den Mitochondrien lokalisiert (Chen, Calvo et al. 2001) und besitzt die Fähigkeit, Mikroporen in einer physiologischen Membran auszubilden und transmembrane Konduktivität zu generieren (Chanturiya, Basanez et al. 2004). Daher kann man davon ausgehen, dass sPB1-F2 vergleichbare biochemische Eigenschaften besitzt wie das virale Protein. Die chemischen Crosslink-Studien belegen, dass der N-terminale (PB-(1-40)) und der Cterminale (PB-(50-87)) Abschnitt von PB1-F2 die inhärente Fähigkeit besitzt zu multimerisieren. Das zentrale Fragment PB-(30-70) zeigt keine Tendenz zur Oligomerisierung, trägt aber durch einen Cystein-Rest in Position 42 zur ausgeprägten Dimerisierung von PB1-F2 bei. In-silico-Analysen zeigten, dass sich eine schwächere Oligomerisierungsdomäne (A.s. 9-13) im N-Terminus und eine starke Domäne (A.s. 68-72) in der C-terminalen Region des Proteins befindet (Bruns, Studtrucker et al. 2007). Dieser Befund stimmt mit den Daten der Crosslink-Studien überein, da die Multimerisierung von PB-(50-87) bereits bei 10fach weniger DSS zu sehen war als für das N-terminale Fragment. Interessanterweise war das C-terminale Fragment in der Lage, mit dem Gesamtlängenprotein (PB1-F21-87) zu interagieren und intermediäre Spezies auszubilden. Dass dieses Ergebnis von biologischer Relevanz sein könnte, wird durch in vivo Daten bestätigt, die aufzeigen, dass nach einer IAVPR8-Infektion von MDCK-Zellen und anschließender radioaktiver 35 S- Markierung neben der 10-kD-Hauptbande eine 6-kD-Spezies zu sehen ist, die als ein Cterminales Fragment von PB1-F2 identifiziert wurde (Zamarin, Ortigoza et al. 2006). Dieses Fragment wird durch ein Start-Codon downstream des ursprünglich beschriebenen Codons von PB1-F2 gebildet und konnte mit dem viralen PB1-F2 koimmunopräzipitiert werden, was mit der in den Crosslink-Studien ermittelten starken Multimerisierungstendenz des Cterminalen Fragmentes übereinstimmt. Weiterhin wurde die starke Tendenz von PB1-F2 zu oligomerisieren auch in dem Kontext seiner pro-apoptotischen Funktion diskutiert (Zamarin, Garcia-Sastre et al. 2005). Neben der Fähigkeit des Proteins, mit beiden Untereinheiten des VDAC zu interagieren, wäre es denkbar, dass es durch Multimerisierung zur Ausbildung von Poren in der mitochondrialen Membran kommt und so die Destabilisierung des Mitochondrienpotentials induziert wird. Sequenzanalysen haben ergeben, dass die Ladungsverteilung innerhalb des helikalen C-Terminus von PB1-F2 diese Voraussetzung erfüllt, indem das Protein in eine kationische, der negativen Membranoberfläche zugewandte 71 Diskussion Seite und eine anionische, sterisch abgewandte Region, die mit einem potentiellen zweiten PB1-F2-Molekül interagiert, eingeteilt werden kann (Bruns, Studtrucker et al. 2007). Die biologische Funktion der PB1-F2-Multimerisierung ist noch nicht geklärt und wird sicherlich noch Gegenstand späterer Untersuchungen sein. Die bisherigen Daten legen die Vermutung nahe, dass PB1-F2 in die Gruppe der Viroporin-Proteine eingeteilt werden kann. Dabei handelt es sich definitionsgemäß um Virusproteine, die den Durchtritt von Ionen und kleineren Molekülen durch Membranen vermitteln (Gonzalez and Carrasco 2003). Sie sind in fast allen Familien zu finden wie z.B. das M2-Protein der Orthomyxoviridae, Vpu vom HIV-1 der Retroviridae oder das 2B-Protein der Picornaviridae. Mit Ausnahme des M2-Proteins sind diese Proteine für den Replikationszyklus meist nicht relevant oder deren Funktion diesbezüglich, ähnlich wie bei PB1-F2, nicht geklärt. Des weiteren besitzt PB1-F2 Ähnlichkeit mit dem mitochondrialen Bax-Protein, einem pro-apoptotischen Vertreter der Bcl-2 Familie, welches ebenfalls oligomere Strukturen ausbildet (Wei, Zong et al. 2001; Chanturiya, Basanez et al. 2004). Leider war es bisher schwierig, PB1-F2-vermittelte-proapoptotische Effekte in Zellkultur zu studieren (Zamarin, Garcia-Sastre et al. 2005; Zamarin, Ortigoza et al. 2006), wodurch neben der Entschlüsselung der molekularen Mechanismen auch die Relevanz des Oligomerisierungsphänomens noch ungeklärt ist. Daher ist es nicht verwunderlich, dass sich in diesem Forschungsbereich in den vergangenen Jahren die deutliche Tendenz abzeichnete, in-vivo-Systeme im Mausmodell zu etablieren, um die Bedeutung dieses Pathogenitätsfaktors zu klären, der immer öfter im Kontext der dramatischen Auswirkungen hochpathogener Isolate erwähnt wird (Conenello, Zamarin et al. 2007; McAuley, Hornung et al. 2007; Basler and Aguilar 2008). 72 Abkürzungen 7. Abkürzungsverzeichnis Abb. Abbildung α Alpha A.s. Aminosäuren Amp Ampicillin ATP Adenosintriphosphat β Beta βME 2-Mercaptoethanol BIM Bisindolylmaleimid bp Basenpaar BS3 bis(sulfosuccinimidyl)suberate BSA Rinderserum Albumin bzw Beziehungsweise °C Grad Celsius Ca2+ Calcium-Ion CK-2 Casein-Kinase-2 CMV Zytomegalovirus ddH2O Doppelt deionisiertes Wasser D-MEM Dulbecco’s modified eagle medium DMSO Dimethylsulfoxid DNA Desoxyribonukleosid-5’ –triphosphat DSS Disuccinimidyl suberate DTT Dithiotreithol ECL enhanced chemoluminescence EGS ethylene glycol disuccinate di(N-succinimidyl)ester FKS Fötales Kälberserum FACS Fluoreszenz-Aktivierter-Zellsortierer g Gramm GA glutaraldehyde h Stunde HA Hämagglutinin H2O2 Wasserstoffperoxid H7 1-(5-Isoquinolinesulfonyl)-2-methylpiperazine IAV Influenza-A-Virus 73 Abkürzungen kDa Kilodalton l Liter Lsg. Lösung µ Mikro µl Mikroliter µCi Mikrocurie µM Mikromolar m Milli M Molar M1 Influenza-Matrix-Protein 1 M2 Influenza-Matrix-Protein 2 MEM Minimal essential medium min Minute ml Milliliter mM Millimolar MOI Multiplicity of infection (infektiöse Viruspartikel pro Zelle) MTS Mitochondriale Lokalisierungssequenz mU Milliunits NA Neuraminidase ng Nanogramm NP Nukleoprotein OD Optische Dichte ORF Open Reading Frame PB1 Influenza „basische Polymerase 1“ PB1-F2 Influenza “basische Polymerase 1, offener Leserahmen 2” PBS Phosphate buffered saline pfu Plaque forming units pH potentia Hydrogenii, Säurestärke PI3 Phosphoinositol-3-Kinase PKC Protein-Kinase C PMA Phorbol-Myristyl-Acetat PR8 Influenza A/Puerto Rico/8/34 (H1N1) PTPC Permeability transition pore complex Rpm Umdrehungen pro Minute 74 Abkürzungen RNP Influenza-Ribonukleoprotein-Komplex RT Raumtemperatur SDS sodium dodecyl sulfate Sek Sekunden sPB1-F2 synthetisches PB1-F2 STS Staurosporin Tab. Tabelle Tris Tris (hydroxymethylmethan) aminomethan ÜN über Nacht VDAC Voltage Dependent Anion Channel Vpr Virales Protein R (HIV) WSN William Smith (Neurotropic), (Virusisolat von 1933) Kurzschreibweise der Aminosäuren: Ala (A) Alanin Gly (G) Glycin Pro (P) Prolin Arg (R) Arginin His (H) Histidin Ser (S) Serin Asp (D) Asparaginsäure Ile (I) Isoleucin Thr (T) Threonin Asn (N) Asparagin Leu (L) Leucin Trp (W) Tryptophan Cys (C) Cystein Lys (K) Lysin Tyr (Y) Tyrosin Glu (E) Glutaminsäure Met (M) Methionin Val (V) Valin Gln (Q) Glutamin Phe (F) Phenylalanin 75 Literaturverzeichnis 8. Literaturverzeichnis Abraham, N., D. F. Stojdl, et al. (1999). "Characterization of transgenic mice with targeted disruption of the catalytic domain of the double-stranded RNA-dependent protein kinase, PKR." J Biol Chem 274(9): 5953-62. Ahmad, Z., F. T. Lee, et al. (1984). "Phosphorylation of glycogen synthase by the Ca2+- and phospholipid-activated protein kinase (protein kinase C)." J Biol Chem 259(14): 87437. Ali, A., R. T. Avalos, et al. (2000). "Influenza virus assembly: effect of influenza virus glycoproteins on the membrane association of M1 protein." J Virol 74(18): 8709-19. Arora, D. J. and N. Gasse (1998). "Influenza virus hemagglutinin stimulates the protein kinase C activity of human polymorphonuclear leucocytes." Arch Virol 143(10): 2029-37. Arrese, M. and A. Portela (1996). "Serine 3 is critical for phosphorylation at the N-terminal end of the nucleoprotein of influenza virus A/Victoria/3/75." J Virol 70(6): 3385-91. Bachi, T., W. Gerhard, et al. (1969). "Morphogenesis of influenza A virus in Ehrlich ascites tumor cells as revealed by thin-sectioning and freeze-etching." J Virol 4(5): 769-76. Balachandran, S., P. C. Roberts, et al. (2000). "Essential role for the dsRNA-dependent protein kinase PKR in innate immunity to viral infection." Immunity 13(1): 129-41. Balachandran, S., P. C. Roberts, et al. (2000). "Alpha/beta interferons potentiate virusinduced apoptosis through activation of the FADD/Caspase-8 death signaling pathway." J Virol 74(3): 1513-23. Barman, S., A. Ali, et al. (2001). "Transport of viral proteins to the apical membranes and interaction of matrix protein with glycoproteins in the assembly of influenza viruses." Virus Res 77(1): 61-9. Barman, S. and D. P. Nayak (2000). "Analysis of the transmembrane domain of influenza virus neuraminidase, a type II transmembrane glycoprotein, for apical sorting and raft association." J Virol 74(14): 6538-45. Basler, C. F. and P. V. Aguilar (2008). "Progress in identifying virulence determinants of the 1918 H1N1 and the Southeast Asian H5N1 influenza A viruses." Antiviral Res 79(3): 166-78. Baum, L. G. and J. C. Paulson (1990). "Sialyloligosaccharides of the respiratory epithelium in the selection of human influenza virus receptor specificity." Acta Histochem Suppl 40: 35-8. Benedict, C. A., P. S. Norris, et al. (2002). "To kill or be killed: viral evasion of apoptosis." Nat Immunol 3(11): 1013-8. Beveridge, W. I. (1991). "The chronicle of influenza epidemics." Hist Philos Life Sci 13(2): 223-34. Blom, N., S. Gammeltoft, et al. (1999). "Sequence and structure-based prediction of eukaryotic protein phosphorylation sites." J Mol Biol 294(5): 1351-62. Blom, N., T. Sicheritz-Ponten, et al. (2004). "Prediction of post-translational glycosylation and phosphorylation of proteins from the amino acid sequence." Proteomics 4(6): 1633-49. Bruns, K., N. Studtrucker, et al. (2007). "Structural characterization and oligomerization of PB1-F2, a proapoptotic influenza A virus protein." J Biol Chem 282(1): 353-63. Bui, M., G. Whittaker, et al. (1996). "Effect of M1 protein and low pH on nuclear transport of influenza virus ribonucleoproteins." J Virol 70(12): 8391-401. Bukrinskaya, A. G., N. K. Vorkunova, et al. (1982). "Influenza virus uncoating in infected cells and effect of rimantadine." J Gen Virol 60(Pt 1): 49-59. Cai, H., U. Smola, et al. (1997). "Role of diacylglycerol-regulated protein kinase C isotypes in growth factor activation of the Raf-1 protein kinase." Mol Cell Biol 17(2): 732-41. 76 Literaturverzeichnis Chanturiya, A. N., G. Basanez, et al. (2004). "PB1-F2, an influenza A virus-encoded proapoptotic mitochondrial protein, creates variably sized pores in planar lipid membranes." J Virol 78(12): 6304-12. Chen, R. and E. C. Holmes (2008). "The Evolutionary Dynamics of Human Influenza B Virus." J Mol Evol. Chen, W., P. A. Calvo, et al. (2001). "A novel influenza A virus mitochondrial protein that induces cell death." Nat Med 7(12): 1306-12. Chu, W. M., D. Ostertag, et al. (1999). "JNK2 and IKKbeta are required for activating the innate response to viral infection." Immunity 11(6): 721-31. Cohen, G. M. (1997). "Caspases: the executioners of apoptosis." Biochem J 326 ( Pt 1): 1-16. Colamussi, M. L., M. R. White, et al. (1999). "Influenza A virus accelerates neutrophil apoptosis and markedly potentiates apoptotic effects of bacteria." Blood 93(7): 2395403. Conenello, G. M. and P. Palese (2007). "Influenza A virus PB1-F2: a small protein with a big punch." Cell Host Microbe 2(4): 207-9. Conenello, G. M., D. Zamarin, et al. (2007). "A single mutation in the PB1-F2 of H5N1 (HK/97) and 1918 influenza A viruses contributes to increased virulence." PLoS Pathog 3(10): 1414-21. Constantinescu, S. N., C. D. Cernescu, et al. (1991). "Effects of protein kinase C inhibitors on viral entry and infectivity." FEBS Lett 292(1-2): 31-3. Cox, N. J. and K. Subbarao (2000). "Global epidemiology of influenza: past and present." Annu Rev Med 51: 407-21. Criswell, B. S., R. B. Couch, et al. (1979). "The lymphocyte response to influenza in humans." Am Rev Respir Dis 120(3): 700-4. D'Agostino, D. M., L. Ranzato, et al. (2002). "Mitochondrial alterations induced by the p13II protein of human T-cell leukemia virus type 1. Critical role of arginine residues." J Biol Chem 277(37): 34424-33. Dong, C., R. J. Davis, et al. (2002). "MAP kinases in the immune response." Annu Rev Immunol 20: 55-72. Ehrhardt, C., T. Wolff, et al. (2007). "Activation of phosphatidylinositol 3-kinase signaling by the nonstructural NS1 protein is not conserved among type A and B influenza viruses." J Virol 81(21): 12097-100. Engelich, G., M. White, et al. (2002). "Role of the respiratory burst in co-operative reduction in neutrophil survival by influenza A virus and Escherichia coli." J Med Microbiol 51(6): 484-90. Erdmann, M., J. Dorrie, et al. (2007). "Effective clinical-scale production of dendritic cell vaccines by monocyte elutriation directly in medium, subsequent culture in bags and final antigen loading using peptides or RNA transfection." J Immunother 30(6): 66374. Falk, K., E. Namork, et al. (1997). "Characterization of infectious salmon anemia virus, an orthomyxo-like virus isolated from Atlantic salmon (Salmo salar L.)." J Virol 71(12): 9016-23. Fesq, H., M. Bacher, et al. (1994). "Programmed cell death (apoptosis) in human monocytes infected by influenza A virus." Immunobiology 190(1-2): 175-82. Fouchier, R. A., V. Munster, et al. (2005). "Characterization of a novel influenza A virus hemagglutinin subtype (H16) obtained from black-headed gulls." J Virol 79(5): 281422. Fujimoto, I., T. Takizawa, et al. (1998). "Co-expression of Fas and Fas-ligand on the surface of influenza virus-infected cells." Cell Death Differ 5(5): 426-31. Gescher, A. (1998). "Analogs of staurosporine: potential anticancer drugs?" Gen Pharmacol 31(5): 721-8. 77 Literaturverzeichnis Ghosh, S., M. J. May, et al. (1998). "NF-kappa B and Rel proteins: evolutionarily conserved mediators of immune responses." Annu Rev Immunol 16: 225-60. Gibbs, J. S., D. Malide, et al. (2003). "The influenza A virus PB1-F2 protein targets the inner mitochondrial membrane via a predicted basic amphipathic helix that disrupts mitochondrial function." J Virol 77(13): 7214-24. Gonzalez, M. E. and L. Carrasco (2003). "Viroporins." FEBS Lett 552(1): 28-34. Gorlich, D., S. Prehn, et al. (1994). "Isolation of a protein that is essential for the first step of nuclear protein import." Cell 79(5): 767-78. Gottlieb, T. A., A. Gonzalez, et al. (1986). "Sorting and endocytosis of viral glycoproteins in transfected polarized epithelial cells." J Cell Biol 102(4): 1242-55. Gottschalk (1959). "Chemistry of Virus Receptors. In The Viruses, Biochemical, Biological and Biophysical properties." Academic Press New York: 51-61. Graham, F. L., J. Smiley, et al. (1977). "Characteristics of a human cell line transformed by DNA from human adenovirus type 5." J Gen Virol 36(1): 59-74. Hay, A. J., B. Lomniczi, et al. (1977). "Transcription of the influenza virus genome." Virology 83(2): 337-55. Henklein, P., K. Bruns, et al. (2005). "Influenza A virus protein PB1-F2: synthesis and characterization of the biologically active full length protein and related peptides." J Pept Sci 11(8): 481-90. Herrler, G. and H. D. Klenk (1991). "Structure and function of the HEF glycoprotein of influenza C virus." Adv Virus Res 40: 213-34. Herz, C., E. Stavnezer, et al. (1981). "Influenza virus, an RNA virus, synthesizes its messenger RNA in the nucleus of infected cells." Cell 26(3 Pt 1): 391-400. Hinshaw, V. S., C. W. Olsen, et al. (1994). "Apoptosis: a mechanism of cell killing by influenza A and B viruses." J Virol 68(6): 3667-73. Hiscott, J., H. Kwon, et al. (2001). "Hostile takeovers: viral appropriation of the NF-kappaB pathway." J Clin Invest 107(2): 143-51. Huang, T. S., P. Palese, et al. (1990). "Determination of influenza virus proteins required for genome replication." J Virol 64(11): 5669-73. Ito, T., Y. Kobayashi, et al. (2002). "Virulent influenza A viruses induce apoptosis in chickens." Virus Res 84(1-2): 27-35. Jackson, R. J. (2005). "Alternative mechanisms of initiating translation of mammalian mRNAs." Biochem Soc Trans 33(Pt 6): 1231-41. Julkunen, I., K. Melen, et al. (2000). "Inflammatory responses in influenza A virus infection." Vaccine 19 Suppl 1: S32-7. Karin, M. and M. Delhase (2000). "The I kappa B kinase (IKK) and NF-kappa B: key elements of proinflammatory signalling." Semin Immunol 12(1): 85-98. Kerr, J. F., A. H. Wyllie, et al. (1972). "Apoptosis: a basic biological phenomenon with wideranging implications in tissue kinetics." Br J Cancer 26(4): 239-57. Kikkawa, U., M. Go, et al. (1986). "Rapid purification of protein kinase C by high performance liquid chromatography." Biochem Biophys Res Commun 135(2): 636-43. Klenk, H. D., Cox, N.J. (1995). Orthomyxoviridae, virus taxonomy. Virus taxonomy. F. A. a. F. Murphy, C.M., Springer-Verlag: 293-9. Klumpp, K., R. W. Ruigrok, et al. (1997). "Roles of the influenza virus polymerase and nucleoprotein in forming a functional RNP structure." Embo J 16(6): 1248-57. Kolch, W., G. Heidecker, et al. (1993). "Protein kinase C alpha activates RAF-1 by direct phosphorylation." Nature 364(6434): 249-52. Korteweg, C. and J. Gu (2008). "Pathology, molecular biology, and pathogenesis of avian influenza A (H5N1) infection in humans." Am J Pathol 172(5): 1155-70. Kozak, M. (1991). "Structural features in eukaryotic mRNAs that modulate the initiation of translation." J Biol Chem 266(30): 19867-70. 78 Literaturverzeichnis Kroemer, G., B. Dallaporta, et al. (1998). "The mitochondrial death/life regulator in apoptosis and necrosis." Annu Rev Physiol 60: 619-42. Kujime, K., S. Hashimoto, et al. (2000). "p38 mitogen-activated protein kinase and c-junNH2-terminal kinase regulate RANTES production by influenza virus-infected human bronchial epithelial cells." J Immunol 164(6): 3222-8. Kunzelmann, K., A. H. Beesley, et al. (2000). "Influenza virus inhibits amiloride-sensitive Na+ channels in respiratory epithelia." Proc Natl Acad Sci U S A 97(18): 10282-7. Kurokawa, M., H. Ochiai, et al. (1990). "Inhibitory effect of protein kinase C inhibitor on the replication of influenza type A virus." J Gen Virol 71 ( Pt 9): 2149-55. Leahy, M. B., J. T. Dessens, et al. (1997). "The fourth genus in the Orthomyxoviridae: sequence analyses of two Thogoto virus polymerase proteins and comparison with influenza viruses." Virus Res 50(2): 215-24. Lee, C. W. and Y. M. Saif (2008). "Avian influenza virus." Comp Immunol Microbiol Infect Dis. Levesque, L., N. M. Dean, et al. (1997). "Antisense oligonucleotides targeting human protein kinase C-alpha inhibit phorbol ester-induced reduction of bradykinin-evoked calcium mobilization in A549 cells." Mol Pharmacol 51(2): 209-16. Li, J. and G. Gobe (2006). "Protein kinase C activation and its role in kidney disease." Nephrology (Carlton) 11(5): 428-34. Lin, C., R. E. Holland, Jr., et al. (2002). "Caspase activation in equine influenza virus induced apoptotic cell death." Vet Microbiol 84(4): 357-65. Lin, C., S. G. Zimmer, et al. (2001). "The involvement of a stress-activated pathway in equine influenza virus-mediated apoptosis." Virology 287(1): 202-13. Lowy, R. J. (2003). "Influenza virus induction of apoptosis by intrinsic and extrinsic mechanisms." Int Rev Immunol 22(5-6): 425-49. Lowy, R. J. and D. S. Dimitrov (1997). "Characterization of influenza virus-induced death of J774.1 macrophages." Exp Cell Res 234(2): 249-58. Ludwig, S., C. Ehrhardt, et al. (2001). "Influenza virus-induced AP-1-dependent gene expression requires activation of the JNK signaling pathway." J Biol Chem 276(24): 10990-8. Ludwig, S., S. Pleschka, et al. (2006). "Ringing the alarm bells: signalling and apoptosis in influenza virus infected cells." Cell Microbiol 8(3): 375-86. Ludwig, S., S. Pleschka, et al. (1999). "A fatal relationship--influenza virus interactions with the host cell." Viral Immunol 12(3): 175-96. Ludwig, S., T. Wolff, et al. (2004). "MEK inhibition impairs influenza B virus propagation without emergence of resistant variants." FEBS Lett 561(1-3): 37-43. Maniatis, T., J. V. Falvo, et al. (1998). "Structure and function of the interferon-beta enhanceosome." Cold Spring Harb Symp Quant Biol 63: 609-20. Marjuki, H., M. I. Alam, et al. (2006). "Membrane accumulation of influenza A virus hemagglutinin triggers nuclear export of the viral genome via protein kinase Calphamediated activation of ERK signaling." J Biol Chem 281(24): 16707-15. Martin, K. and A. Helenius (1991). "Nuclear transport of influenza virus ribonucleoproteins: the viral matrix protein (M1) promotes export and inhibits import." Cell 67(1): 117-30. Matlin, K. S., H. Reggio, et al. (1981). "Infectious entry pathway of influenza virus in a canine kidney cell line." J Cell Biol 91(3 Pt 1): 601-13. Matrosovich, M. N., T. Y. Matrosovich, et al. (2004). "Human and avian influenza viruses target different cell types in cultures of human airway epithelium." Proc Natl Acad Sci U S A 101(13): 4620-4. Mazur, I., D. Anhlan, et al. (2008). "The proapoptotic influenza A virus protein PB1-F2 regulates viral polymerase activity by interaction with the PB1 protein." Cell Microbiol. 79 Literaturverzeichnis McAuley, J. L., F. Hornung, et al. (2007). "Expression of the 1918 Influenza A Virus PB1-F2 Enhances the Pathogenesis of Viral and Secondary Bacterial Pneumonia." Cell Host & Microbe 2(4): 240-49. McCullers, J. A. (2006). "Insights into the interaction between influenza virus and pneumococcus." Clin Microbiol Rev 19(3): 571-82. Mori, I., T. Komatsu, et al. (1995). "In vivo induction of apoptosis by influenza virus." J Gen Virol 76 ( Pt 11): 2869-73. Morse, M. A., A. C. Marriott, et al. (1992). "The glycoprotein of Thogoto virus (a tick-borne orthomyxo-like virus) is related to the baculovirus glycoprotein GP64." Virology 186(2): 640-6. Muthumani, K., D. S. Hwang, et al. (2002). "HIV-1 Vpr induces apoptosis through caspase 9 in T cells and peripheral blood mononuclear cells." J Biol Chem 277(40): 37820-31. Nakano, H., E. Kobayashi, et al. (1987). "Staurosporine inhibits tyrosine-specific protein kinase activity of Rous sarcoma virus transforming protein p60." J Antibiot (Tokyo) 40(5): 706-8. Nath, S. T. and D. P. Nayak (1990). "Function of two discrete regions is required for nuclear localization of polymerase basic protein 1 of A/WSN/33 influenza virus (H1 N1)." Mol Cell Biol 10(8): 4139-45. Nichols, J. E., J. A. Niles, et al. (2001). "Human lymphocyte apoptosis after exposure to influenza A virus." J Virol 75(13): 5921-9. Nicholson, D. W., A. Ali, et al. (1995). "Identification and inhibition of the ICE/CED-3 protease necessary for mammalian apoptosis." Nature 376(6535): 37-43. Nieto, A., S. de la Luna, et al. (1994). "Complex structure of the nuclear translocation signal of influenza virus polymerase PA subunit." J Gen Virol 75 ( Pt 1): 29-36. Nishikawa, M., H. Hidaka, et al. (1983). "Phosphorylation of smooth muscle heavy meromyosin by calcium-activated, phospholipid-dependent protein kinase. The effect on actin-activated MgATPase activity." J Biol Chem 258(23): 14069-72. Oda, T., T. Akaike, et al. (1989). "Oxygen radicals in influenza-induced pathogenesis and treatment with pyran polymer-conjugated SOD." Science 244(4907): 974-6. Oh, S. and M. C. Eichelberger (2000). "Polarization of allogeneic T-cell responses by influenza virus-infected dendritic cells." J Virol 74(17): 7738-44. Olsen, C. W., J. C. Kehren, et al. (1996). "bcl-2 alters influenza virus yield, spread, and hemagglutinin glycosylation." J Virol 70(1): 663-6. Pahl, H. L. (1999). "Activators and target genes of Rel/NF-kappaB transcription factors." Oncogene 18(49): 6853-66. Pahl, H. L. and P. A. Baeuerle (1995). "Expression of influenza virus hemagglutinin activates transcription factor NF-kappa B." J Virol 69(3): 1480-4. Paine, P. L. (1975). "Nucleocytoplasmic movement of fluorescent tracers microinjected into living salivary gland cells." J Cell Biol 66(3): 652-7. Patskan, G. J. and C. S. Baxter (1985). "Specific stimulation of histone H2B and H4 phosphorylation in mouse lymphocytes by 12-O-tetradecanoylphorbol 13-acetate." J Biol Chem 260(24): 12899-903. Patterson, S., J. Gross, et al. (1988). "The intracellular distribution of influenza virus matrix protein and nucleoprotein in infected cells and their relationship to haemagglutinin in the plasma membrane." J Gen Virol 69 ( Pt 8): 1859-72. Patterson, S., J. S. Oxford, et al. (1979). "Studies on the mechanism of influenza virus entry into cells." J Gen Virol 43(1): 223-9. Pearson, G., F. Robinson, et al. (2001). "Mitogen-activated protein (MAP) kinase pathways: regulation and physiological functions." Endocr Rev 22(2): 153-83. Pinto, L. H., L. J. Holsinger, et al. (1992). "Influenza virus M2 protein has ion channel activity." Cell 69(3): 517-28. 80 Literaturverzeichnis Planz, O., S. Pleschka, et al. (2001). "MEK-specific inhibitor U0126 blocks spread of Borna disease virus in cultured cells." J Virol 75(10): 4871-7. Pleschka, S., T. Wolff, et al. (2001). "Influenza virus propagation is impaired by inhibition of the Raf/MEK/ERK signalling cascade." Nat Cell Biol 3(3): 301-5. Pringle, C. R. (1998). "Virus taxonomy--San Diego 1998." Arch Virol 143(7): 1449-59. Privalsky, M. L. and E. E. Penhoet (1981). "The structure and synthesis of influenza virus phosphoproteins." J Biol Chem 256(11): 5368-76. Razvi, E. S. and R. M. Welsh (1995). "Apoptosis in viral infections." Adv Virus Res 45: 1-60. Regenmortel, v. (2000). Virus taxonomy: the classification and nomenclature of viruses, San Diego: Academic Press. Richardson, J. C. and R. K. Akkina (1991). "NS2 protein of influenza virus is found in purified virus and phosphorylated in infected cells." Arch Virol 116(1-4): 69-80. Roach, P. J. (1991). "Multisite and hierarchal protein phosphorylation." J Biol Chem 266(22): 14139-42. Roder, R., K. Bruns, et al. (2008). "Synthesis of full length PB1-F2 influenza A virus proteins from 'Spanish flu' and 'bird flu'." J Pept Sci 14(8): 954-62. Root, C. N., E. G. Wills, et al. (2000). "Entry of influenza viruses into cells is inhibited by a highly specific protein kinase C inhibitor." J Gen Virol 81(Pt 11): 2697-705. Ruegg, U. T. and G. M. Burgess (1989). "Staurosporine, K-252 and UCN-01: potent but nonspecific inhibitors of protein kinases." Trends Pharmacol Sci 10(6): 218-20. SAMBROOK (1989.). Molecular cloning: A laboratory manual, Cold Spring Harbor Laboratory Press. Samuel, C. E. (2001). "Antiviral actions of interferons." Clin Microbiol Rev 14(4): 778-809, table of contents. Sanz-Ezquerro, J. J., J. Fernandez Santaren, et al. (1998). "The PA influenza virus polymerase subunit is a phosphorylated protein." J Gen Virol 79 ( Pt 3): 471-8. Scheiffele, P., A. Rietveld, et al. (1999). "Influenza viruses select ordered lipid domains during budding from the plasma membrane." J Biol Chem 274(4): 2038-44. Schubert, U., T. Schneider, et al. (1992). "Human-immunodeficiency-virus-type-1-encoded Vpu protein is phosphorylated by casein kinase II." Eur J Biochem 204(2): 875-83. Schultz-Cherry, S., N. Dybdahl-Sissoko, et al. (2001). "Influenza virus ns1 protein induces apoptosis in cultured cells." J Virol 75(17): 7875-81. Schultz-Cherry, S. and V. S. Hinshaw (1996). "Influenza virus neuraminidase activates latent transforming growth factor beta." J Virol 70(12): 8624-9. Sedger, L. M., S. Hou, et al. (2002). "Bone marrow B cell apoptosis during in vivo influenza virus infection requires TNF-alpha and lymphotoxin-alpha." J Immunol 169(11): 6193-201. Sherman, M. P. and W. C. Greene (2002). "Slipping through the door: HIV entry into the nucleus." Microbes Infect 4(1): 67-73. Sherman, M. P., U. Schubert, et al. (2002). "HIV-1 Vpr displays natural protein-transducing properties: implications for viral pathogenesis." Virology 302(1): 95-105. Sieczkarski, S. B., H. A. Brown, et al. (2003). "Role of protein kinase C betaII in influenza virus entry via late endosomes." J Virol 77(1): 460-9. Silic-Benussi, M., I. Cavallari, et al. (2004). "Suppression of tumor growth and cell proliferation by p13II, a mitochondrial protein of human T cell leukemia virus type 1." Proc Natl Acad Sci U S A 101(17): 6629-34. Skehel, J. J. and D. C. Wiley (2000). "Receptor binding and membrane fusion in virus entry: the influenza hemagglutinin." Annu Rev Biochem 69: 531-69. Suarez, D. L. and S. Schultz-Cherry (2000). "Immunology of avian influenza virus: a review." Dev Comp Immunol 24(2-3): 269-83. 81 Literaturverzeichnis Suzuki, Y., T. Ito, et al. (2000). "Sialic acid species as a determinant of the host range of influenza A viruses." J Virol 74(24): 11825-31. Sweet, C. and H. Smith (1980). "Pathogenicity of influenza virus." Microbiol Rev 44(2): 30330. Takeda, M., G. P. Leser, et al. (2003). "Influenza virus hemagglutinin concentrates in lipid raft microdomains for efficient viral fusion." Proc Natl Acad Sci U S A 100(25): 14610-7. Takizawa, T., K. Ohashi, et al. (1996). "Possible involvement of double-stranded RNAactivated protein kinase in cell death by influenza virus infection." J Virol 70(11): 8128-32. Tamaoki, T., H. Nomoto, et al. (1986). "Staurosporine, a potent inhibitor of phospholipid/Ca++dependent protein kinase." Biochem Biophys Res Commun 135(2): 397-402. Taniguchi, T. and A. Takaoka (2002). "The interferon-alpha/beta system in antiviral responses: a multimodal machinery of gene regulation by the IRF family of transcription factors." Curr Opin Immunol 14(1): 111-6. Taubenberger, J. K., A. H. Reid, et al. (2000). "The 1918 influenza virus: A killer comes into view." Virology 274(2): 241-5. Taubenberger, J. K., A. H. Reid, et al. (2001). "Integrating historical, clinical and molecular genetic data in order to explain the origin and virulence of the 1918 Spanish influenza virus." Philos Trans R Soc Lond B Biol Sci 356(1416): 1829-39. Taubenberger, J. K., A. H. Reid, et al. (2005). "Characterization of the 1918 influenza virus polymerase genes." Nature 437(7060): 889-93. Thornberry, N. A. and Y. Lazebnik (1998). "Caspases: enemies within." Science 281(5381): 1312-6. Toker, A. (1998). "Signaling through protein kinase C." Front Biosci 3: D1134-47. Toth, R., E. Szegezdi, et al. (1999). "Regulation of cell surface expression of Fas (CD95) ligand and susceptibility to Fas (CD95)-mediated apoptosis in activation-induced T cell death involves calcineurin and protein kinase C, respectively." Eur J Immunol 29(2): 383-93. Toullec, D., P. Pianetti, et al. (1991). "The bisindolylmaleimide GF 109203X is a potent and selective inhibitor of protein kinase C." J Biol Chem 266(24): 15771-81. Tumpey, T. M., X. Lu, et al. (2000). "Depletion of lymphocytes and diminished cytokine production in mice infected with a highly virulent influenza A (H5N1) virus isolated from humans." J Virol 74(13): 6105-16. Warrilow, D., J. Gardner, et al. (2006). "HIV type 1 inhibition by protein kinase C modulatory compounds." AIDS Res Hum Retroviruses 22(9): 854-64. Webb, B. L., S. J. Hirst, et al. (2000). "Protein kinase C isoenzymes: a review of their structure, regulation and role in regulating airways smooth muscle tone and mitogenesis." Br J Pharmacol 130(7): 1433-52. Webby, R. J. and R. G. Webster (2001). "Emergence of influenza A viruses." Philos Trans R Soc Lond B Biol Sci 356(1416): 1817-28. Webster, R. G., W. J. Bean, et al. (1992). "Evolution and ecology of influenza A viruses." Microbiol Rev 56(1): 152-79. Wei, M. C., W. X. Zong, et al. (2001). "Proapoptotic BAX and BAK: a requisite gateway to mitochondrial dysfunction and death." Science 292(5517): 727-30. Weiss, A., R. L. Wiskocil, et al. (1984). "The role of T3 surface molecules in the activation of human T cells: a two-stimulus requirement for IL 2 production reflects events occurring at a pre-translational level." J Immunol 133(1): 123-8. 82 Literaturverzeichnis Woodgett, J. R., K. L. Gould, et al. (1986). "Substrate specificity of protein kinase C. Use of synthetic peptides corresponding to physiological sites as probes for substrate recognition requirements." Eur J Biochem 161(1): 177-84. Wright, P. F. a. W., R.G. (2001). Orthomyxoviruses. Philadelphia, Lippincott Williams and Wilkens. Wurzer, W. J., O. Planz, et al. (2003). "Caspase 3 activation is essential for efficient influenza virus propagation." Embo J 22(11): 2717-28. Wyllie, A. H., J. F. Kerr, et al. (1980). "Cell death: the significance of apoptosis." Int Rev Cytol 68: 251-306. Yamada, H., R. Chounan, et al. (2004). "Mitochondrial targeting sequence of the influenza A virus PB1-F2 protein and its function in mitochondria." FEBS Lett 578(3): 331-6. Yewdell, J. and A. Garcia-Sastre (2002). "Influenza virus still surprises." Curr Opin Microbiol 5(4): 414-8. Zamarin, D., A. Garcia-Sastre, et al. (2005). "Influenza virus PB1-F2 protein induces cell death through mitochondrial ANT3 and VDAC1." PLoS Pathog 1(1): e4. Zamarin, D., M. B. Ortigoza, et al. (2006). "Influenza A virus PB1-F2 protein contributes to viral pathogenesis in mice." J Virol 80(16): 7976-83. Zell, R., A. Krumbholz, et al. (2007). "Prevalence of PB1-F2 of influenza A viruses." J Gen Virol 88(Pt 2): 536-46. Zhirnov, O. P., T. E. Konakova, et al. (1999). "Caspase-dependent N-terminal cleavage of influenza virus nucleocapsid protein in infected cells." J Virol 73(12): 10158-63. Zhirnov, O. P., T. E. Konakova, et al. (2002). "NS1 protein of influenza A virus downregulates apoptosis." J Virol 76(4): 1617-25. Zhirnov, O. P., A. L. Ksenofontov, et al. (2002). "Interaction of influenza A virus M1 matrix protein with caspases." Biochemistry (Mosc) 67(5): 534-9. Zitzow, L. A., T. Rowe, et al. (2002). "Pathogenesis of avian influenza A (H5N1) viruses in ferrets." J Virol 76(9): 4420-9. 83 Danksagung Danksagung Herrn Prof. Dr. Ulrich Schubert möchte ich für die Betreuung der Promotionsarbeit herzlichst danken. Besonders hervorheben möchte ich dabei seine fachliche Unterstützung bei der Erstellung der Veröffentlichung dieser Arbeit sowie die großartigen Rahmenbedingungen, die einen erfolgreichen Abschluss der Promotion ermöglicht haben. Herrn Prof. Dr. Bernhard Fleckenstein danke ich für die Möglichkeit zur Promotion am Institut für Klinische und Molekulare Virologie. Herrn Prof. Dr. Andreas Burkovski danke ich für seine Bereitschaft zur Begutachtung dieser Arbeit. Ebenso danke ich dem Prüfungsvorsitzenden Hr. Prof. Dr. Fritz Titgemeyer, dem Vorsitzenden der Prüfungskomission Prof. Dr. Eberhard Bänsch für die Genehmigung der Promotion sowie Herrn PD Dr. Robert Slany für die Bereitschaft zur Prüfung. Mein ganz besonderer Dank gilt Frau Nicole Studtrucker für die experimentelle Einarbeitung und Unterstützung im Rahmen dieser Promotion. Ihr kollegiales und freundliches Verhalten sowie die zahlreichen wissenschaftlichen Diskussionen waren eine wertvolle Hilfe. Weitherhin möchte ich mich bei Herrn Prof. Dr. Stephan Ludwig sowie seinen Mitarbeitern Dr. Igor Mazur, Dr. Anhlan Darisuren, Frau Sabine Dudek sowie Frau Ludmilla Wixler für eine großartige Kooperation bedanken, die entscheidend zum Erfolg dieser Arbeit beigetragen hat. In gleicher Weise möchte ich Dr. Peter Henklein, Herrn Rene Roeder, Dr. Viktor Vray, Herrn Karsten Bruns, Dr. Josef Wissing und Herrn Uwe Tessmer danken. Meinen Kollegen vom Institut für Klinische und Molekulare Virologie sowie den Kollegen der Virologik GmbH in Erlangen danke ich für die freundliche Zusammenarbeit und die schöne Zeit, die wir gemeinsam verbringen konnten. Für die fachliche Unterstützung und Diskussion danke ich ganz besonders Herrn Dr. Andreas Goldwich, Herrn Jörg Votteler, PD Frank Neipel, Herrn Friedrich Hahn, Herrn André Eißman, Frau Annette Maczurek, Frau Danijela Cvijetic, Herrn Torsten Walther, Frau Jana Pforr, Frau Sabine Hahn, Frau Liane Neumann und Frau Ingrid Hercegfi und Herrn Dr. Völk. Vielen Dank auch meinen Eltern, Geschwistern und Freunden, die mir in dieser Zeit immerwährend zur Seite standen. 84 Lebenslauf Geburtsdaten: Familienstand: Staatsangehörigkeit: Schulbildung 1981 – 1982 1982 – 1987 09/1987 – 06/1992 09/1992 – 07/1996 Zivildienst 11/1996-10/1997 Studium 11/1997-06/2003 10/2003-06/2007 Seit 07/2007 16.06.1975 in Lichtenfels (Bayern) ledig deutsch Deutsche Grundschule Bagdad, Irak. Pater Lunkenbein Volksschule in Ebensfeld. Staatliche Realschule in Staffelstein. Abschluss: Mittlere Reife (kaufm. Zweig). Gymnasium Theresianum in Bamberg. Abschluss: Abitur (Note 2,0) Malteser Hilfsdienst in Bamberg Biologie Friedrich-Alexander-Universität in Erlangen Hauptfach: Biochemie. Diplomarbeit (November AG, Erlangen): Thema: „Molekularbiologischer und immunologischer Nachweis von Oligomeren in einem technischen System“ Abschluss: Diplom Biologe Note: 1,2 Promotion am Institut für Klinische und Molekulare Virologie, der Friedrich-AlexanderUniversität in Erlangen. Abschluss der Promotion in der ViroLogik GmbH in Erlangen, Koordination des Projektbereichs Influenza und Evaluierung antiviraler Substanzen in Erlangen. Publikationen: Bruns, K., N. Studtrucker, et al. (2007). "Structural characterization and oligomerization of PB1-F2, a proapoptotic influenza A virus protein." J Biol Chem 282(1): 353-63. Mazur, I., D. Anhlan, et al. (2008). "The proapoptotic influenza A virus protein PB1-F2 regulates viral polymerase activity by interaction with the PB1 protein." Cell Microbiol. David Mitzner, Igor Mazur, et al. (2008). „Phosphorylation of the influenza A virus PB1-F2 protein by PKC is required for efficient virus propagation.”Cell Microbiol. Eingereichte Publikation. 85