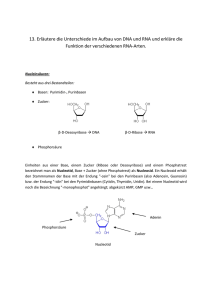
Vorlesung Prof. Nissler WS
Werbung

Vorlesung Prof. Nissler WS 2002 Molekularbiologie 1. Pyrimidin- und Purin-Stoffwechsel 2. DNA- und RNA-Struktur 3. Biochemie von Zellzyklus und Apoptose 4. Replikation 5. Mutationen und Reparatur 6. Gentechnik 7. Transkription 8. Posttranskriptionale Modifikation der RNA 9. Transkriptionsregulation 10. Translation 11. Proteinfaltung 12. Post- und cotranslationale Modifikation von Proteinen 13. Intrazellulärer Transport von Proteinen 14. Intrazelluläre Proteolyse 15. Biochemie der Viren 16. Cancerogenese 17. Gentherapie 1. Pyrimidin- und Purin-Stoffwechsel Chemie der Pyrimidin- und Purinbasen: Numerierung, Pyrimidinbasen: Cytosin, Uracil, Thymin; Purinbasen: seltene Basen: 5-Methylcytosin (in Pflanzen), Pseudouridin, Lactim/Lactamtautomerie Purinbasen: Adenin, Guanin, Hypoxanthin, Xanthin, Basencharakter, Nucleosid = Base + Pentose, N-glykosidische Bindung, Cytosin Cytidin; Thymin Thymidin; Uracil Uridin; Adenin Adenosin; Guanin Guanosin; Hypoxanthin Inosin; Xanthin Xanthosin Nukleotid = Base + Pentose + Phosphat AMP = die Adenosinmonophosphorsäure heißt Adenylsäure, ihre Salze sind die Adenylate GMP = Guanosinmonophosphorsäure, Guanylsäure, Guanylate Vorkommen von Nukleotiden außerhalb der DNA und der RNA energiereiche Phosphate (ATP) cyclische Monophosphate als Signalstoffe (cAMP) Bausteine gruppenübertragender Coenzyme (NAD, FAD, Coenzym A, Cobalamin, "aktives Sulfat", "aktives Methionin"); als Säureanhydride zur Aktivierung von Bausteinen für Biosynthesen (UDP-Glucose, Cytidindiphosphatcholin) Stoffwechsel der Pyrimidinbasen: Synthese: Ausgangsstoffe sind Aspartat und Carbamylphosphat, Carbamylphosphat-Synthese: extramitochondrial durch Carbamylphosphatsynthetase II aus Gln und HCO3(intramitochonadrial durch Carbamylphosphatsynthetase I aus NH3 und HCO3-: Harnstoffsynthese) Synthese des Pyrimidin-Rings Produkt: Orotat Anlagerung von PRPP (Phosphoribosylpyrophosphat führt zum Nukleosid OMP, Decarboxylierung von OMP liefert UMP Cytidin-Synthese: 2 x Phosphorylierung (2 ATP) zu UTP, Anlagerung der NH2-Gruppe von Glutamin an C4 ergibt CTP. Herkunft der Ribose: aus der Nahrung oder Glucosestoffwechsel ( Pentosephosphatcyclus) Thymin-Synthese: Thy kommt nur in der DNA vor. Ausgangsmaterial = UMP: Überführung in Desoxyribonucleotid, Anlagerung der Methylgruppe von Methylentetrahydrofolsäure (Stoffwechsel der C1-Fragmente) auf C5 durch Thymidylatsynthase Synthese der Desoxyribonucleotide: Die Pymidin- und Purin-Nucleosid-Monophosphate werden mit ATP phosphoryliert. Auf der Stufe der Nukleosiddiphosphate erfolgt die Entfernung der C2´-OH-Gruppe durch die Ribonukleotid-Reduktase. dATP ist ein allosterischer Inhibitor des Enzyms (ADA-Mangel!) Regulation: negative allosterische Rückkopplungshemmung der Carbamylphosphatase II durch UTP allosterische Aktivierung der Carbamylphosphatsynthetase II durch PRPP Abbau: Der Abbau erfolgt durch Ringspaltung zu ß-Ala bzw. ß-Aminobutyrat, Endprodukte: CO2, NH3, Acetat bzw. Propionat Stoffwechsel Purinbasen Synthese: Ausgangsstoff: Ribose-5-P (aus Pentosephosephatcyclus, Nahrung) wird zu PRPP aktiviert, dann wird die NH2-Gruppe von Gln, die das künftige N9 der Base ist, mit dem C1´-Atom der Ribose verbunden. Ausgehend von diesem N9 erfolgt die Synthese des Prurin-Rings unter Beteiligung von Gln, Gly, Formyl-TH4, Gln, CO2, Asp, und noch einmal Formyl-TH4, Produkt ist das Nukleotid IMP AMP wird aus IMP durch Anlagerung der Aminogruppe von Asp an C6 synthetisiert. GMP wird aus IMP durch Anlagerung der Aminogruppe von Gln an C2 synthetisiert, nachdem IMP zu Xanthosinphosphat (NAD-abhängig) oxidiert wurde. Die Modifikation der Purinbasen findet also auf der Stufe der Nukleosidmonophosphate statt, die der Pyrimidine auf der Stufe der Nukleosidtriphosphate. Der Energiebedarf ist mit 6 (für Ade) und 7 (für Gua) ATP sehr hoch (210 kJ/mol). Regulation: Rückkopplungshemmungen (PRPP-pyrophosphokinase, PRPP-Amidotransferase); stöchiometrische Kopplung Abbau: Nukleotidasen spalten P vom C5´-Monoester ab. Nukleosidphosphorylasen spalten die C1´-N9-Bindung. Oxidation der Purinbasen nach Entfernung der Zucker wird mit Xanthinoxydase zu Hypoxanthin bzw. Xanthin und Harnsäure. Harnsäureausscheidung: 4-6 mmol Urat/Tag im Harn ( S3). Entstehung von Superoxidradikalen (O2-) bei der Xanthinoxidasereaktion Wiederverwertung freier Pyrimidin- und Purinbasen (Bergungsstoffwechsel, Salvage-Wege) ist sinnvoll und wichtig, weil der Energiebedarf für die Purinsynthese sehr hoch ist. Es gibt zwei Phosphoribosyltransferasen: eine für Ade und eine für Hyp/Gua. Alle Purinnukleotide hemmen die PRPP-Transferasen Purinnukleotidcyclus (AMP IMP + NH3 (+ Asp) AMP + Fumarat) sorgt z.B. dafür, daß bei schwerer Muskelarbeit das in hoher Konzentration anfallende AMP nicht in den Abbauweg einmündet (Dephosphorylierung zu Adenosin). Für Pyrimidine ist noch nichts genaues bekannt. Pathobiochemie des Purinstoffwechsels 1. primäre Hyperuricämie (Gicht): Harnsäurespiegel ( 0.4 mmol/ Serum) und in allen Geweben gekennzeichnet (6 mmol 180 mmol/d)). - renale Ursachen: tubuläre Harnsäuresekretion (75% aller Fälle) - Fehlen der Salvage-Enzyme - Überaktivität der PRPP-Synthetase. - Adenin-Phosphoribosyltransferase fehlt (LESCH-NYHAN-Syndrom): Gicht + neurologische Symptome 2. sekundäre Hyperuricämie: Nucleinsäureumsatz Überproduktion von Urat, Nukleotidstoffwechsel OK - myeloischen Leukämien, Psoriasis, G-6-Pase-Mangel (G-6-P PPC = PRPP) - Antimetabolittherapie, Zytostatika bei Malignomen führt zur Hemmung der DNASynthese auch in anderen rasch proliferierenden Geweben. (Folsäureantagonisten, Inhibitor der Dihydrofolatreduktase: Amino und Amethopterin, Inhibitor der Thymidylatsynthase: 5-F-Uracil ( S25). - Virostatika: Acyclovir wird von der viralen Thymidinkinase zu ACV-Triphosphat phosphoryliert, das eine 30-fach höhere Affinität zur Virus-DNA-Polymerase hat und zum Kettenabbruch führt. Gancyclovir wird von der zelleigenen Gua-kinase umgesetzt und führt auch zum Kettenabbruch. 3. Adenosindesaminasemangel führt in Lymphozyten zu einer Erhöhung des dATPSpiegels, der ein starker Inhibitor der Ribonukleotidreduktase ist ( S2). Damit wird die DNA-Synthese u.a. auch in B- und T-Zellen gehemmt, was zu einem schweren Immundefekt führt. Therapie der Gicht: diätetisch, Uricosuria, Allopurinol 2. DNA- und RNA-Struktur DNA: Doppelstrang aus Desoxyribonucleotiden, RNA: Einzelstrang aus Ribonucleotiden DNA Polymerisation als 3',5' Phosphodiester, in der RNA sind auch 2',3' Diester möglich und vorkommend. Doppelstrang aus zwei antiparallelen Desoxyribonucleotidsträngen, die durch H-Brückenbildung zwischen den Basen nichtkovalent zusammengehalten werden. Voraussetzung: Lactim/Lactamtautomerie (wenn nicht die Ketoform vorliegt, kann es zu Fehlablesungen kommen) CHARGAFF's Regeln (Pyr:Pur = 1:1, G:C=1:1, A:T=1:1), das Verhältnis der AT-Paare zu den GC-Paaren ist etwa 1.3. WATSON und CRICK schlugen 1953 das Modell der Doppelhelix vor, das mit den hydrophilen Phosphatgruppen außen und den Basen innen der Struktur der Proteine entspricht. B-Konformation ist die häufigste (rechtsgängig), die A-Form ist artifiziell (dehydratisiert, als RNA-DNA-Hybrid vorkommend)), und die Z-Form ist linksgängig und kommt selten (in GCreichen Abschnitten) vor. Stabilisierung durch H-Brücken. Schmelzen der DNA = durch Erwärmen bedingtes Auseinanderweichen der beiden Stränge, das um so leichter geht, je mehr AT-Paare enthalten sind. bakterielle und mitochondriale DNA sind ringförmig, haben also keine freien Enden Größe der DNA, Säurecharakter, Ladungsneutralisierung Konturlänge der DNA beschreibt die Länge des DNA-Fadens bei Annahme eines linaren Makromoleküls. Sie ist bei E. coli 1.36 m und beim Menschen 1.8 µm. Chromatin: DNA des Zellkerns in kondensierter Form assoziiert mit Histonen Histone (H2A, H2B, H3, H4) = basische Proteine (MG 11 - 23 kDa), reich an Lys und Arg, hochkonserviert. Histone schirmen die anionischen Ladungen der DNA ab und bilden mit den entsprechenden DNA-Abschnitten zusammen das Nukleosom: Unterste Organisationsebene des Chromatins, gebildet von einem oktameren Histon-Core und ca. 150 bp. Zwischen den Nukleosomen liegen 50- 60 bp lange Abschnitte (linker-DNA) von variabler Länge. Die Nukleosomenstruktur wird durch Histon H1 stabilisiert. Bei der Transcription muß bei der Aktivierung der Chromosomenabschnitte die Kondensierung aufgehoben werden. Die NH2-Termini der Core-Histone der Nucleosomen werden durch Acetyltransferasen und Deacetylasen reversibel acetyliert ( S18). Dadurch ändert sich die Polarität und die Affinität zur DNA, die strukturstabilisierende Wirkung wird reversibel aufgehoben und es enstehen lokale Auflockerungen. Heterochromatin = hochkondensiertes Chromatin, bleibt auch im Interphasekern kondensiert, und damit anfärbbar, transkriptionell inaktiv Euchromatin = lockeres, diffuses Chromatin Nichthistonproteine bilden das Gerüst für lange DNA-Schlaufen. Das Gerüst entspricht einem Metaphase-Chromosom. Eines der beiden Proteine ist die Topoisomerase II ( S8). Nichthistonproteine sind auch die verschiedenen Transkriptionsfaktoren. Gen = gesamte Nukleinsäuresequenz, die zur Synthese eines funktionsfähigen Polypeptids oder RNA-Moleküls notwendig ist. Die genetische Information ist nicht kontinuierlich entlang der Nucleotid-Sequenz aufgereiht, sondern wird durch informationslose Nucleotidsequenzen unterbrochen. Exon = Genabschnitt, der exprimierende Sequenz enthält. Intron = Genabschnitt, der nicht Aminosäuren codiert, intervenierende Sequenz, die zwei Exons voneinander trennt. Single-copy-Gene = exprimierende Sequenz, die im haploiden Chromosomensatz nur 1 x vorkommt (25 - 50% aller DNA-Abschnitte) repetitive DNA = DNA-Sequenzen, die in einem Chromosom mehrfach auftreten tandemartig wiederholte Genabschnitte codieren für Transkripte, die schnell in großer Konzentration gebraucht werden (z.B. für Histone, rRNA). Minisatelliten-DNA = vielfache Wiederholungen einfacher DNA-Abschnitte, deren Anzahl individualspezifisch ist und zur Bestimmung des genetischen Fingerabdrucks benutzt werden ( S11). Transposons, Retroposons, SINES und LINES (short and long interspersed elements). sind bewegliche DNA-Elemente, die für die Vielfalt der Antikörper und der T-Zell-Rezeptoren verantwortlich sind. Genfamilien entstehen durch Verdopplungen (z.B.: Immunglobuline). Pseudogene stellen Verdopplungen dar, die funktionslos geworden sind. Allele = alternative (sich ausschließende) Formen eines Gens, die sich in homologen Chromosomen an gleicher Stelle befinden Chromosomen: Lichtmikrokopisch sichtbare Gebilde, durch basische Farbstoffe anfärbbar. Charakteristisches Bandenmuster dient aber der Orientierung (z.B. bei der Identifizierung von Brüchen oder Doppelungen). G-Banden entstehen nach Färbung mit Giemsa, Q-Banden nach Färbung mit Quinacrin. Centromer = Kreuzungspunkt (Konstriktion) eines Metaphase-Chromosoms, and dem die Mitosespindel bindet, p ist der kurze, q der lange Arm. Polytäne Chromosomen enthalten das gleiche Strukturgen mehrfach (Drosophila). Telomeren sind die Enden der Chromosomen, die beim Menschen Polymere der Sequenz 5' TTAGGG 3' enthalten. Aus den Versuchen, künstliche Chromosomen herzustellen (YACs, von yeast artificial chromosomes) wurde klar, daß zur Replikation drei Elemente nötig sind: Replikationsursprung, Centromere und Telomere, die Telomeren bilden am Ende des DNAFadens Schleifen, die vor Exonuklease-Abbau schützen. Telomerasen sind RNA-Protein-Komplexe (Enzyme), die die Länge der Telomeren konstant halten. Sie sind nur in malignen Tumoren und in embryonalem Gewebe aktiv ( S9). Prokaryonten haben ein ringförmiges Chromosom mit einem einzigen Replikationsursprung bleibt auch im Interphasekern kondensiert Diploid bedeutet, daß jedes Chr. 2 x vorhanden ist. Die Replikation der DNA findet in der S-Phase der Mitose statt. RNA 1. heterogene nucleäre RNA (hnRNA): primäres Transkriptionsprodukt 2. Messenger-RNA: entsteht aus hnRNA, (= Matrize bei Proteinsynthese) ( S12) 3. Tranfer-RNA (t-RNA): Bindung der Aminosäure, Transfer zum Proteinsyntheseapparat ( S15) 4. ribosomale RNA: Strukturelement bei der Ribosomen-Assemblierung ( S15) 5. kleine nucleäre RNA (small nuclear RNA, snRNA): assoziiert an Protein, Bestandteil des Speißosoms, spleißt hnRNA ( S13) 6. kleine cytoplasmatische RNA (scRNA): assoziiert an Protein (SRC) 7. mitochondriale RNA 8. Virale RNA (vRNA) ( S21) 3. Biochemie von Zellzyklus und Apoptose G0-Phase: die meisten ausdifferenzierten Zellen befinden sich in der G0-Phase, d.h. sie teilen sich nicht mehr, wie z.B. Neuronen oder Zellen der Augenlinse, sie haben den Zellzyklus verlassen. Zellen können aus der G0-Phase durch den Einfluß von Wachstumsfaktoren in die G1-Phase übergehen. G1-Phase: G für gap = Lücke, postmitotische Ruhephase, dauert bei einer sich rasch teilenden menschlichen Zelle (wie z.B. Epithelien) rund 4 - 10 Stunden. Biochemisch ist sie durch RNA- und Proteinsynthese sowie durch Größenzunahme der Zelle gekennzeichnet. Synthese von Histonen, Enzymen, die in der S-Phase zur Replikation/Transkription benötigt werden, Hormonen. In der G1-Phase liegt ein wichtiger Kontrollpunkt, der den Beginn der S-Phase determiniert, von dem aus es kein zurück in die G0-Phase mehr gibt. S-Phase (Synthese-Phase), ca. 8 Stunden, in ihr findet die Synthese von DNA, RNA, Enzymen (Replikation) statt, Bildung des Centrosoms. G2-Phase: prämitotische Ruhephase ca. 12 Stunden, es werden die Proteine für die Mitose synthetisiert. In G2 wird kontrolliert, ob die gesamte DNA repliziert ist, ansonsten verharrt die Zelle in G2 und tritt nicht in die M-Phase ein. G1, S, G2 werden als Interphase zusammengefaßt. M-Phase oder Mitose: Prophase: Auflösung der Kernmembran durch Phosphorylierung von Lamin, das dadurch depolymerisiert, Kondensation der Schwesterchromatiden, Ausbildung der Zellpole, der Kinetochoren und des Spindelapparates Prometaphase: die Chromosomen wandern zur Äquatorialplatte Metaphase: Anordnung an der Äquatorialplatte Anaphase: Trennung der Schwesterchromatiden an dem Centromer und Bewegung zum Zellpol, der Mechanismus der Bewegung entlang der Kinetochoren ist noch nicht aufgeklärt. Telophase: Chromosomen entwinden sich, Kondensation nimmt ab, Neubildung der Kernmembran, Abbau des mitotischen Cyclins. Zytokinese: Verteilung des Zytosols auf beide Tochterzellen. Kontrolle des Zellzyklus 1. Proteinkinasen (Cyclin-abhängig, CDK, cyclin dependent proteinkinase), Proteinphosphatasen, cyclusabhängig exprimiert. Interphase , Mitosephase 2. Cycline = Regulatorische Untereinheiten der Proteinkinasen, die den Zellzyklus kontrollieren. Expression in Interphase , Mitosephase , danach proteolytischer Abbau 3. Prolyl-Peptidyl-cis/trans-Isomerase Check-Points des Zellzyklus 1. G0 G1 Kontrolle durch Wachstumsfaktoren, durch die Zellen einen Restriktionspunkt der G1Phase überschreiten. Nach dem Durchlaufen des "point of no return", von dem aus Wachstumsfaktoren nicht mehr nötig sind, werden vor allem Transkriptionsfaktoren der Familie E2F synthetisiert ( S12). E2F aktiviert die Transkription der mRNA für Proteine, die für die DNA-Synthese benötigt werden, also z.B. DNA-Polymerasen. Ohne Wachstumsfaktoren, Substratmangel und durch andere Signale können können Zellen aus der G1 in die G0-Phase eintreten, in der sie lange. u.U. lebenslang verbleiben. 2. G1 S Kontrolle durch Tumorsuppressor-Gen p53 (Chromosom 17) p53-Protein (393 AS). p53 = Transkriptionsfaktor Bei Schädigung der Erbanlagen (Mutationen in der DNA ( S8)) wird die Expression des p53-Gens erhöht: zelluläre [p53-Protein] erhöht ( S24). Folge: Blockierung des Zellzyklus in der G1-Phase, Induktion der Enzyme der DNAReparatur ( S9), Einleitung der Apoptose = Aufrechterhaltung der genetischen Integrität Mechanismus: eine spezifische DNA-abhängige Proteinkinase erkennt mutierte DNA, bindet an die Enden der mutierten DNA und phosphoryliert das p53Protein (2 x) Aktivierung des p53-Proteins. Reaktion von p53 mit einem weiteren Tumorsupressor-Gen-(ing 1)-Produkt, dem p33ING1-Protein [p53/p33ING1-Protein]-Komplex bindet an DNA an p21 Gen Expression von p21-Gen = p21-Protein p21-Protein = Cyclin-abhängiger Inhibitor von Proteinkinasen, der die Zellproliferation auf der Stufe der G1-Phase hemmt. p21-Proteinkinase-Inhibitor hemmt cyclinabhängige Proteinkinase. Dadurch wird das Genprodukt des Retinoblastoma-Suszeptibilitäts-Gens (Chromosom 13, 928 AS), das Retinoblastoma-Protein (= Tumorsuppressorprotein) nicht phosphoryliert nicht phosphoryliertes Retinoblastoma-Protein bindet Transkriptionsfaktor E2F, dadurch kann E2F nicht proliferierend wirken, Übergang von G1 S wird verhindert 3. G2 M Kontrolle durch 1. Maturation-promoting factor (MPF, reifungsfördernder Faktor) = Komplex von Proteinkinase p34cdc2 (katalytische Subeinheit) und Cyclin B (regulatorische SE) p34 kann durch vielfältige Mechanismen aktiviert und inaktiviert werden; unterliegt damit einer genauen Kontrolle. Die aktive Proteinkinase phosphoryliert in der Mitosephase zahlreiche Kernproteine ( Auflösung der Kernmembran, Chromosomendekondensation, Spindelbildung) Histone, RNA-Polymerase II, Laminine A,B,C, Vimentin, Caldesmon und Transkriptionsfaktoren. 2. Pin 1: Prolyl-Peptidyl-cis/trans-Isomerase ( S17). Bremst Einsetzen der Mitose (pinning down) isomerisiert Peptidbindungen, die vor einem Prolyrest liegen, in CDK-abhänigig phosphorylierten Proteinen. Verhindert vorzeitige Zellteilung. Pathobiochemie Mutationen im p 53-Gen, die zur Inaktivierung der Tumorsuppressorfunktion führen, lassen Zellen in die nachfolgenden Phasen eintreten, obwohl die DNA fehlerhaft ist. Man findet in sehr vielen Tumoren p53-Mutationen: Carcinome (Missense-Typ), Sarcome (Deletionen, Insertionen ( S9,24) Mutationen im Retinoblastomgen-Produkt kommt in Retinoblastomen (Netzhauttumoren), kleinzelligen Bronchialcarcinomen Osteosarcomen usw. vor. Ausfall von Rb führt zur malignen Transformation der Zellen: Inhibitorwirkung von Rb auf Transkriptionsfaktor E2F fällt weg. Apoptose (Programmierter Zelltod): Biologischer Hintergrund: Die Zellzahl eines Organs wird durch Proliferation und Zelluntergang reguliert. Die Notwendigkeit einer solchen Regulation besteht in der Entwicklungsphase, aber auch später spielen sich in vielen Geweben ständig Umbauvorgänge ab. So ist die Apoptose auch für das Gleichgewicht im Immunsystem notwendig, z.B. für die Selbsttoleranz. Apoptose ist die häufigste Form von Zelltod im Organismus. Sie wird durch folgende biochemische/zellbiologische Charakteristika morphologisch definiert: - Verlust der Stabilität der Plasmamebran, Ausstülpungen (Zeiose) - Abschnüren von membranumschlossenen Vesikeln (Blebbing) - Verlust der Membranasymmetrie (Exposition von Phosphatidylserin nach außen) - Schrumpfen des Kerns, Chromatinkondensation, - DNA-Fragmentierung durch Wirkung von Endonukleasen zwischen den Nukleosomen; - apoptotische Zellen / deren Überreste werden von Makrophagen (CD14-Receptor) phagocytiert; daher keine Entzündungsreaktion - Vakuolisierung des Cytoplasmas Der Unterschied zur Nekrose besteht in folgendem: - bei der Nekrose schwellen Zellen an und platzen - der Zellinhalt incl. Zellorganellen wird demzufolge nach außen abgegeben - dem folgt wiederum eine Entzündungsreaktion - die Nekrose ist nicht energieabhängig, Apoptose ist energieabhängig Apoptose-auslösende Faktoren: Signale von außen: Tumornekrosefaktor (TNF , Viren, z.B. Adenoviren, Wegfall von ZellZell-Kontakt, Fas-Ligand, Ceramid u.a.m.. Die Zytokine binden an Rezeptoren, die eine sog. Todesdomäne besitzen. Die Bindung des Liganden induziert häufig eine Trimerisierung des Rezeptors, was dann intrazellulär eine Kaskade von Effekten anschaltet. Der am besten untersuchte Rezeptor ist das Molekül CD95 (CD steht für geclusterte, d.h. an einem Fleck in der Membran konzentrierte Domäne) Signale von innen: Onkogene, p53, Retinoblastomprotein, Cytochrom, Effektoren: Apoptose-auslösende Faktoren setzen eine Kaskade der Aktivierung von Proteasen (Caspasen) in Gang. Caspasen sind Killerproteinasen, die den Suicidreaktionsweg katalysieren. Es gibt 10 verschiedene Caspasen, die in inaktiven Vorstufen (Procaspasen) vorliegen und durch limitierte Proteolyse autocatalytisch, durch andere Caspasen, durch Calpaine und Cathepsine aktiviert werden. Es wird bei den Caspasen zwischen Initiator- und Exekutier-Caspasen unterschieden, erstere stehen am Anfang, letztere am Ende der Aktivierungskaskade. Caspasen sind hochaktive Cystein-Proteasen, z.B. das Interleukin 1 converting enzyme (ICE alter Name) = Caspase 1, die hochselektiv Proteine spalten mit einer Spezifität gegenüber Asp, das hinter einem Tetrapeptid sitzen muß (Cysteinyl-aspartat-spezifische Proteinasen). Substrate sind DNA-Reparatur-Enzyme, Prä-m-RNA-Spleiß-Enzyme, Kontrollproteine der Steroidbiosynthese, Tumorsuppressorproteine, Zelladhäsionsproteine, Poly-ADP-RibosePolymerase, Actin, Lamin, Huntingtin. 4. Mechanismus der Replikation Replikation erfolgt semikonservativ vom 5'- zum 3'- Ende durch DNA-abhängige DNAPolymerase. Diese benötigt einzelsträngige DNA als Matritze (template), die Nucleosidtriphosphate als Substrate und Primer. Primer (RNA) sind erforderlich, da die DNA-Polymerasen nur bereits vorhandene Sequenzen durch Anheftung der Nukleotide an das 3´-OH-Ende verlängern können, sie werden durch eine RNA-Polymerase (Primase) synthetisiert. In der Initiationsphase weichen die beiden Stränge der DNA-Helix auseinander, es entstehen an vielen Stellen Replikationsblasen mit je zwei Replikationsgabeln (Replikons). Nach Primer-Synthese (RNA-Starterstrang) erfolgt in der Elongationsphase die DNA-Synthese (100 bp/sec mit rund 10.000 - 100.000 Replikationsgabeln) durch die DNA-Polymerasen I, II und III (Prokaryonten) bzw. DNA-Polymerasen (Eukaryonten) Die Synthese erfolgt vom 5´- zum 3´-Ende, die Ableserichtung ist 3´ 5´. Infolge der antiparallelen Anordnung beider DNA-Stränge erfolgt die Replikation am Leitstrang (= Führungsstrang = leading strand, der Strang der DNA-Doppelhelix, der von 3' 5' läuft) in einem Stück in Richtung der Bewegung der Replikationsgabel () und am Folgestrang (= Verzögerungsstrang, = lagging strand, der Strang der Helix, der von 5' 3' läuft) in entgegengesetzter Richtung. Die Synthese am Folgestrang erfolgt bruchstückweise (OKAZAKI-Fragmente) durch . Der DNA-Polymerase /Primase-Komplex startet die Synthese am Leitstrang, danach am Folgestrang. Die RNA-Primer werden durch die 5´ 3´ Exonuklease-Aktivität der DNA-Polymerase I (Prokaryonten) bzw. der Ribonuclease H (Eukaryonten) entfernt. Die entstandenen Lücken werden durch die DNA-Polymerase 1 bzw. aufgefüllt. Die Verknüfung der komplettierten Stränge erfolgt durch die DNA-Ligase mit ATP oder NAD+ als Energie-Donator. Die DNA-Polymerasen I und II bzw. , und haben Korrekturlesefähigkeit und verfügen über 3´ 5´-Exonuklease-Aktivität, die der Reparatur dient. Das Auseinanderweichen der DNA-Stränge der Doppelhelix erfolgt bei der Replikationsblasenbildung durch die Helicase, die die Wasserstoffbrückenbindungen zwischen den Basenpaaren A-T; C-G löst (die Öffnung einer Bindung erfordert 2 ATP). Zur Entspiralisierung öffnet die Topoisomerase I einen der beiden Stränge, gestattet die Torsion und verschließt ihn wieder. Die Topoisomerase II (DNA-Gyrase) spaltet beide Stränge. Single strand DNAbinding proteins (ssbp) verhindern die Reassoziation. Syntheserichtung: Durch eine Schleifenbildung des Folgestrangs kann trotz Antiparallelität das Polymerase-Dimer (III) bzw. gleichzeitig die Synthese beider Tochterstränge in der gleichen Richtung (bei verkürzten Positionswechseln) katalysieren. Die DNA-Synthese in einer Replikationsblase erfolgt an beiden Gabeln (bidirektional). Der Replikationsstart erfolgt an genau festgelegtem Ort: Consensus-Sequenz (z. B. OriC) mit Hilfe von Initiatorproteinen. Die Termination vermitteln Terminatorproteine. Telomere: Die Chromosomen-Enden des Menschen tragen die repetitive Sequenz 5´-TTGGGG-3´, die bei der Replikation nach Primerentfernung im Folgestrang verkürzt werden. Telomerasen (Ribonucleoprotein, reverse Transcriptasen) synthetisieren diese Sequenz mit Hilfe gebundener RNA als Matrize. Tumoren weisen eine erhöhte TelomeraseAktivität auf. 5. Mutationen und Reparatur Mutationen = Genomveränderungen, vererbbar. nicht durch Trennung von Allelpaaren oder durch Rekombination vorhandener Gene hervorgerufen Genom-Mutation: Änderung der Chromosomenzahl Chromosomen-Mutation: Änderung der Struktur einzelner Chromosomen Gen-Mutation: Änderung an Einzelgenen: Gesamtgen oder einzelne Genorte = Punktmutationen: 1. Substitution: Transition: Austausch von Purinbasen A/G oder Pyrimidinbasen C/U (z.B. Thymin-Tautomerie) Transversion: Austausch von Purinbasen gegen Pyrimidinbase (z.B. HbS, Desaminierungen von Basen) 2. Deletion: Verlust einer Base 3. Insertion: Einbau einer zusätzlichen Base Auswirkung von Substitutionen: 1. Sense-Mutationen: Genprodukt (Protein) ist phänotypisch gesund, Information des Codons ist nicht verändert (WOBBLE-Position); ausgetauschte AS verursacht keinen Struktur- bzw. Funktionsverlust 2. Missense-Mutation: synthetisiertes Protein ist biologisch inaktiv (immunologisch nachweisbar) 3. Nonsense-Mutation: Es wir kein Protein synthetisiert; Aminosäure-Codon ist in ein StopCodon mutiert Auswirkungen von Deletionen/Insertionen: Rastermutation: schwere Veränderungen im Protein, falsches/verstümmeltes Protein (immunologisch nicht nachweisbar) Die Mutationen können in einem oder in beiden Allelen auftreten und sie können rezessiv oder dominant sein. Bei einer rezessiven Mutation tritt der Phänotyp erst in Erscheinung, wenn beide Allele mutiert sind (homozygot). Folgende Schäden in der DNA-Doppelhelix treten auf: Purin-Verluste (ca. 12 000 pro Zelle und Tag) Doppelstrangbrüche ( ca. 9 pro Zelle und Tag) Cytosindesaminierungen (ca. 200 pro Zelle und Tag) Pyrimidinverluste (ca. 600 pro Zelle und Tag) Einzelstrangbrüche (ca. 55 000 pro Zelle und Tag) Pyrimidindimerisation Quervernetzungen zwischen den beiden Strängen (ca. 8/Zelle und Tag) Reparatur: Phasen der Reparatur: - Erkennen (noch nicht geklärt) - Öffnen des Doppelstranges durch eine Endonuklease - Entfernung des beschädigten Stranges durch eine Exonuklease-Aktivität - Verschluß durch Polymerase und Ligase. Reparaturmechanismen: - Nukleotid-Excisionsreparatur (Thymindimer) - Basenexzisionsreparatur (Uracil-Entfernung) - Basenfehlpaarungsreparatur - direkte Reparatur (Methylguanin) - Doppelstrangbruchkorrekturen: kompliziert, da Matritze fehlt! Rekombination Durch crossing over und homologe Rekombination können zwischen homologen Chromosomen ganze Genblöcke ausgetauscht werden. Bei sexueller Fortpflanzung ist die Rekombination ein normaler Prozeß während der Meiose. Sie sind die Ursache für die genetische Vielfalt, die wir beobachten. Die Verschiebung solcher Elemente (Transposons und Retrotranspo-sons) hat nicht die Homologie von Donor- und Akzeptormolekül zur Voraussetzung. Retro-transposons enstehen, wenn zunächst ein DNA-Abschnitt in RNA und danach wieder durch eine reverse Transkriptase in DNA umgeschrieben wird. So können Pseudogene entstehen, denen regulierbare Elemente oder Introns fehlen. Reparatur von Doppelstrangbrüchen durch genetische Rekombination: benutzt wird das Schwesterchromatid als Matrize in der G2-Phase Bei DNA-Schädigung steigt die intrazelluläre Konzentration an Rekombinationsfaktoren und Reparaturenzymen an (SOS-Antwort auf RNA-Schädigung). Mechanismus: Proteolytischer Abbau von Proteinen, die die Gene der Reparaturproteine reprimieren (LexA). Pathobiochemie: Xeroderma pigmentosum: Sonnenlichtüberempfindlichkeit mit Neigung zu Hauttumoren. Mutationen in 7 Genen können zu dieser Erkrankung führen. Betroffen sind z.B. Proteine, die der Erkennung von UVinduzierten DNA-Läsionen dienen und die Reparatureigenschaften stören. Ataxia teleangiectatica Das ATM-Genprodukt (ca. 300 kD) aktiviert nach UV-Bestrahlung das p53-Protein. Bei Mutationen fällt dessen Zellzykluskontrollfunktion aus. 6. Gentechnik (ausgewählte Kapitel) Alle gentechnischen Verfahren beruhen darauf, fremde DNA in Zellen oder Organismen zu bringen und die darin enthaltene Information zur Expression zu bringen. 1. Gentransfer Um DNA handhaben zu können, muß man die großen Moleküle zunächst zerkleinern. Dazu dienen Nucleasen (Phosphodiesterasen, Desoxyribonucleasen, Endonucleasen) Restriktionsendonukleasen sind bakterielle Enzyme, sie führen zur Restriktion, d. h. zur Zerstörung, fremder DNA-Moleküle und schützen damit das Bakterium vor eingedrungener Fremd-DNA. Die Basen der Bak-terien-DNA wird durch spezifische Methylasen modifiziert. Das schützt die eigene DNA vor Abbau durch die Restriktionsendonucleasen, fremde DNA aber nicht. Restriktionsendonucleasen spalten ortsspezifisch an palindromischen Sequenzen. Isolierte und gereinigte Restriktionsendonukleasen dienen in der Gentechnik als Instrumente, um DNA-Stücke herzustellen, deren Enden definiert sind. Dadurch ist das Klonieren: von DNA möglich: Herstellen größerer Mengen identischer DNA (Klone). Die gesuchte DNA-Sequenz wird in einen Vector eingebaut: doppelsträngige DNA-Trägermoleküle, mit denen die Fremd-DNA in eine Zielzelle eingeschleust und dort zur Replikation gebracht wird (Klonierungsvector). Vectoren sind Plasmide: ringförmige, bakterielle DNA-Moleküle. Rekombinante DNA = Konstrukt aus Fremd-DNA und Vector. Konstrukt-Herstellung: Ausschneiden der Fremd-DNA aus der Ursprungs-DNA, z. B. mit Eco RI, Aufschneiden des Vectors (Polyklonierungsstelle) mit Eco RI, Hybridisierung, Ligierung (Ringschluß). Einschleusen in Bakterienzellen = Transformation oder tierische Zellen = Transfection Maßgeschneiderte Vectoren, u.a. Expressionsvectoren sind so konstruiert, daß Bakterienzellen/eukaryote Zellen in die Lage versetzt werden, mit ihrem Proteinsyntheseapparat das Strukturgen in ein funktionsfähiges Protein umzusetzen. So hergestellte Proteine bezeichnet man als rekombinante Proteine. 2. Gewinnung und Klonierung eines Gens Herstellung einer genomischen Genbank: Fragmentierung isolierter DNA einer Zellpopulation mit Restriktionsenzymen, Einbau in Vectoren, Transfektion und Vermehrung von Empfängerzellen, Identifikation spezifischer Genabschnitte mit Gen-Sonden: artifiziell hergestellte DNA-Stücke oder Oligonukleotide von meist 15 - 30 Basenpaaren Länge, die farblich oder radioaktiv markiert werden und zu definierten DNAoder RNA-Sequenzen komplementär sind und deshalb mit diesen Bereichen hybridisieren können. Als Hybridisierung bezeichnet man die Ausbildung von H-Brücken zwischen komplementären Nukleinsäureabschnitten. Zur Herstellung solcher Sonden benötigt man die korrekte Nukleo-tidfolge des zu identifizierenden Nukleinsäurestrangs. Problem Splicing, Introns ( S13). Herstellung einer cDNA-Bank (complementary DNA): Isolierung der RNA, DNA-Synthese mit RNA-abhängiger DNA-Polymerase (reverse Transcriptase) Gentechnische Herstellung von Peptiden und Proteinen: Beispiel Insulin 3. DNA-Sequenzierung: Siehe Praktikumsanleitung S. 74 Das im Herbst 2000 abgeschlossene Humangenomprojekt hat als Ergebnis eine Grobkartierung des gesamten menschlichen Genoms. Mit Hilfe von genetischen Kopplungsanalysen lassen sich damit heute viele Krankheitsursachen auf molekulare Dispositionen zurückführen und daraus Therapiestrategien ableiten ( S25). 4. Polymerase-Kettenreaktion (PCR) Amplifizierung repetitiver Sequenzen von genomischer DNA aus Mund-Epithelzellen. Siehe Praktikumsanleitung S. 78 5. Ortsgerichtete, Oligonucleotid-gesteuerte Mutagenese Verwendung eines chemisch synthetisierten Oligonuclotides, das partiell komplementär ist, in dem eine Base eines Codons gegen eine andere ausgetauscht ist. Da nur eine Base nicht komplementär ist kommt es zur Hybridisierung des "mismatch"-Primers. 6. Fingerprint-Technik Amplifizierung repetitiver DNA (Satelliten-DNA) der zu untersuchenden, genomischen DNA mit PCR. Diese Regionen unterscheiden sich in ihrer Sequenz besonders deutlich von einem Individuum zu anderen. Die selektive Amplifizierierung dieser definierten DNA-Abschnitte erfolgt durch die Auswahl entsprechender Primer. Anschließend erfolgt der Verdau mit Restriktionsendonucleasen und die elektrophoretische Auftrennung der Spaltprodukte (Fragmente). Das Muster der resultierenden Restriktionsfragmente ist für einen Menschen hochspezifisch und vererbbar. (Siehe Praktikumsanleitung) Anwendung der Untersuchung des RestriktionsFragmentLängenPolymorphismus (RFLP): Täteridentifikation, Vaterschaftsnachweis, Mutationsanalyse. 7. Ausschaltung von Genen Blockierung des Expression von Genen: Schutz vor viralen Genen (Infektionen, AIDS) oder Onkogenen Antisense-RNA: Transfektion mit einem Vektor, der das auszuschaltende Gen in umgekehrter Orientierung enthält (= codogener Strang der DNA hat damit dieselbe Polarität wie die mRNA) antisense RNA = komplementär zur mRNA Hybridisierung von antisense RNA und mRNA zum Doppelstrang, der nicht zur Translation taugt und abgebaut wird. Homologe Rekombination: Die DNA mit der Sequenz des auszuschaltenden Gens wird so verändert, daß es funktionslos ist: es wird ein Resistenzgen für das Antibiotikum Neomycin eingebaut. Das Konstrukt enthält keinen Promotor für dieses Gen. Durch Rekombination kann dieses Gen in das Wirtsgenom eingebaut werden. Nur dann, wenn die Rekombination so erfolgt, daß dieses funktionslose Gen an die Stelle des urpsrünglichen, gesunden Gens gelangt, kommt es unter die Wirkung des Promotors und wird repliziert. Durch Neomycin können die Zellen selektioniert werden. 8. Transgene Tiere Ausstattung von Organismen mit vererbbaren, neuen Eigenschaften durch DNA-Injektion in Eizellen. 7. Mechanismus der Transkription Transkription = Herstellung eines einzelsträngigen RNA Moleküls. Dabei dient der MinusStrang als Matrize. Bei der Transkription wird wie bei der Replikation der DNADoppelstrangs entwunden: durch Topoisomerasen. 3 Phasen: Initiation, Elongation und Termination. Promotoren ermöglichen die Bindung der DNA-abhängigen RNA-Polymerasen an den Transkriptionsstartpunkt und regulieren die Effizienz der Transkription. Bei der Termination verhindern bestimmte Strukturen, daß nicht-codierende Bereiche transkribiert werden. RNA-Polymerasen brauchen im Gegensatz zu den DNA-Polymerasen keine Primer. Transkription in Prokaryonten: RNA-Polymerase (2´; ;) Inhibitoren: Aktinomycin D (interkalierend, zwängt sich zwischen die beiden Stränge der DNA-Doppelhelix) Rifampicin hemmt die RNA-Polymerase bei Prokaryonten Transkription in Eukaryonten: 3 RNA-Polymerasen, davon transkribiert die R I im Nukleolus die ribosomale RNA, die R II im Kern die hn (heterogene nukleäre) RNA (größte), die R III im Kern die 5S- und die tRNA. Für die Bindung der RNA-Polymerasen sind Transkriptionsfaktoren (diese sind bei Eukaryonten sehr gross, bis zu 500 kD) nötig. Alle drei Polymerasen bilden unterschiedliche Initiationskomplexe und haben spezielle Transkriptionsfaktoren (mit römischen Zahlen bezeichnet: TF I, II und III). Im Promotorbereich liegen AT-reiche Stellen, die als TATA-Boxen bezeichnet werden. Beim Übergang von der Initiation zur Elongation werden die Polymerasen phosphoryliert. Sie tragen C-terminal ein hochrepetitives Heptapeptid (YSPTSPS), das unter ATP-Verbrauch phosphoryliert wird und damit die Bindung zu den Transkriptionsfaktoren löst. Inhibitor: -Amanitin (das Gift des Knollenblätterpilzes) hemmt die Polymerase II bes. in der Leber. 8. Posttranskriptionale Modifikationen der RNA Aufbereitung (Prozessing) des Primärtranskriptes mRNA Capping: Das 5'-Ende erhält schon während der Transkription eine Kopfgruppe (7-methylguanosintriphosphat). Bedeutung: Stabilität (Schutz vor Nucleasen), Transport aus Kern, Spleißen, Stimulation der Translation Polyadenylierung: Das 3'-Ende enthält ein poly-A-Stück (50-200 Adenylreste), Anheftung nicht am Ende des Pimärtranskriptes, Zielsequenz (AAUAAA) für Anheftung der Poly-APolymerase. Bedeutung für die Stabilität der mRNA; erhöht t/2. Spleißen: Im Gegensatz zu Prokaryonten, bei denen die Strukturgene nacheinander ohne Unterbrechung angeordnet sind, ist die Anordnung bei Eukayonten-DNA diskontinuierlich: Die Protein codierenden Sequenzen (Exons) werden durch Introns, das sind nicht-codierende DNA-Bereiche unterbochen, die zwar mit transkribiert werden, aber funktionslos sind. Sie müssen entfernt werden, sie kommen in der reifen mRNA nicht mehr vor. Introns sind typisch für höhere Eukaryonten, sie finden sich nicht in Hefe und einfachen Einzellern, auch nicht in Prokaryonten. Die Basensequenz eines Introns beginnt mit GU und endet mit AG. Das ist wichtig für das exakte Ausschneiden der vielen Introns. Spleißen ist das Herausschneiden der Introns aus dem Primärtranskript (Prä-mRNA). Spleißosom: Assoziation der Prä-mRNA unter Schleifenbildung (Lassostruktur (engl. lariat) mit Nukleoproteinen (snRNA), die den Spleißvorgang katalysieren. Spleißen ist keine Hydrolyse von Phosphodiesterbildung mit nachfolgender Ligierung, sondern das Ergebnis von zwei aufeinanderfolgenden Umesterungen. Ribozyme: Katalytisch wirksame RNA, Selbstkatalyse ohne Protein: RNA bildet eine Sekundärstruktur und dadurch ein lokale Mikromilieus, das einem aktiven Zentrum von Enzymen ähnlich die Umesterungsreaktionen ermöglicht. Wichtiges Cosubstrat ist ein freies Guanosinmolekül. Der Transport der mRNA aus dem Kern erfolgt selektiv (ungespleißte RNA bleibt drin) und ist unidirektional. Es existiert eine Reihe von Bindungsproteinen dafür ( S19). Der Abbau der mRNA beginnt in Regel durch Deadenylierung (Verlust des poly-A-Schwanzes) und wird durch Ribonukleasen fortgesetzt. Zusätzliche Signale in der 3'-nicht-translatierten Region können zur Stabilisierung beitragen. tRNA entsteht aus einem langen Transkript durch RNAse P, einem Ribozym. Außerdem müssen noch Basen modifiziert werden. Es gibt 40 - 50 verschieden tRNA's, außerdem wird an alle tRNA-Moleküle identisch ein CCA-Triplett addiert, an das die Aminosäure bindet ( S15). rRNA entsteht aus einem 4 Mio bp langen Transkript, das umfangreich methyliert wird. rRNA-Gene sind tandemartig angeordnet. Die rRNA-Synthese findet im Nukleolus statt ( S15). 9. Die Transkriptionsregulation "house keeping genes" werden konstitutiv transkribiert (z.B. Aktin), sie kommen in fast allen Zellen in nahezu identischer Konzentration vor, andere werden induziert. Induktion: selektive Steigerung der Transkription einzelner Gen durch Induktoren, Repression: Hemmung der Transkription einzelner Gene, Rolle von Repressoren. Bei Prokaryonten gilt das Operonmodell (bei Eukaryonten nicht). Ein Repressor bindet an die regulatorische Einheit, die unmittelbar vor dem Transkriptionsstartpunkt liegt, er wird durch einen Induktor aus dieser "hemmenden" Bindung entfernt (lacOperon). Bei Synthesewegen (Beispiel: Tryptophan-Synthese (trp-Operon) in Mikoorganismen. Try ist für den Mensch essentiell) blockiert die Anwesenheit des Endproduktes, Tryptophan, das erste Enzym der Synthesekaskade und gibt den Weg frei, wenn die Konzentration des Endproduktes sinkt, auch das kann wieder über einen Repressor geregelt werden. Try hat die Funktion eines Corepressors. Gen-Regulations-Proteine können an die DNA binden und spezifische Regionen erkennen, ohne daß die Doppelhelix entwunden wird. Bei Eukaryonten ist das alles viel komplizierter. Die Regulation kann an verschiedenen Stufen erfolgen. 1. Aktivierung und Inaktivierung von Genen Aktivierungen/Inaktivierungen werden durch Methylierungen von Cytosin (neben G) in den Kontrollregionen der Gene durch eine spezifische Methyltransferase realisiert. Methylierte DNA-Abschnitte werden nicht mehr transkribiert, das Methylierungsmuster wird bei der Replikation weitergegeben. Die Aktivierung kann zeitlich auf einen bestimmten Entwicklungsabschnitt begrenzt sein. Die Aktivierung kann auch örtlich begrenzt werden. Durch das genomische imprinting wird z.B. festgelegt, welches der beiden Allele ( S4), das väterliche oder das mütterliche, für die Transkription genutzt wird. Beispiel: Nur väterliches Insulin like growth factor-2-Gen wird transcribiert; das Gen ist in Oocyten-DNA methyliert, in Spermatozoen-DNA nicht. In der befruchteten Eizelle ist nur das väterlicher Gen aktiv 2. Regulation der Initiation, "trans-Aktivierung" In Eukaryoten-Genen gibt es regulatorische DNA-Sequenzen, die die Promotoraktivität von Strukturgenen verstärken oder bremsen können. Die Verstärkerregionen auf der DNA (Enhancer) bzw. hemmend wirkenden Regionen (Silencer) werden als cis-aktivierende Elemente bezeichnet. Sie haben selbst keine Promotoraktivität, treten aber mit Promotoren in Wechselwirkungen (Voraussetzung: Schleifenbildung), sie liegen häufig weit stromauf vom Promotor und sind meist nicht größer als 20 bp. Die Aktivierung der cis-aktivierenden Elemente durch Trankriptions-reguliernde Faktoren wird als trans-Aktivierung bezeichnet. Die transkriptionsregulierenden Faktoren (Transaktivatoren) sind diffusible induzierbare (aktivierbare) DNA-bindende Proteine, die immer drei Domänen haben: eine für die DNABindung, eine für die Ligandenbindung (z.B. Hormone) und eine, die den Initiationskomplex der Transkription stabilisiert. Beispiele: Steroidrezeptoren, Thyroid-, Vitamin-, Retinoid-Rezeptoren, c-AMP. cAMP ist nicht nur sekundärer Botenstoff, sondern beeinflußt auch Transkription: die bei hohem cAMP-Spiegel freigesetzte kalaytische Untereinheit der Proteinkinase dringt in den Kern ein, phosphoryliert dort das CRE-Bindungsprotein. Phosphoryliertes CREBP bindet an das CRE (cAMP responsive Element). Als häufig beobachtete DNA-bindende Motive in diesen Proteinen sind Zinkfinger (Cys2-Cys2 oder Cys2-His2), Leuzinzipper (-reißverschluß) Helix-loop-Helix-Motive 3. Variation durch mRNA-Editierung Als RNA-Editing wird die Tatsache bezeichnet, dass durch Basenaustausch in der mRNA veränderte Proteine entstehen können. Synthese von Apolipoprotein B-100 in der Leber, in Mucosa Apo B-48 (kürzer, enthält 48 % der Aminosäuren von Apo B-100) Ursache: Die nur im Darm vorkommende Desaminase desaminiert Cytidin am Codon 2153 CAA zu UAA Stop-Codon. Das Protein ist kürzer, aber trotzdem funktionstüchtig. 4. Alternatives Spleissen und Exon-Skipping: Alternatives Spleißen bedeutet, dass eine RNA an verschiedenen Stellen gespleißt werden kann und dann zu unterschiedlichen mRNA-Arten und auch zu unterschiedlichen Translationsprodukten (Proteinen) führen kann. Je nach Lage der Stellen können ganze Exons "herausfallen", das wird dann als Exonskipping bezeichnet. Beispiel: Tropomyosinformen verschiedener Gewebe 5. Regulation des Transportes aus dem Kern Hierüber ist wenig bekannt. hnRNA wird nicht aus dem Kern transportiert, d.h. der Transport gelingt erst nach Vollendung der Spleißreaktion ( S18). 6. Regulation des Abbaus Für die Geschwindigkeit des Abbaus ist offenbar die Länge des am 3'-Ende befindlichen poly-A-Stückes verantwortlich. Nicht polyadenylierte RNA ist extrem labil und unterliegt dem raschen Abbau durch RNAasen. 7. Die 5' UTR beteiligen sich an der positionellen Transkriptionsregulation, indem sie die Lokalisation des Transkripts in der Zelle bestimmen. Auch hierüber ist noch nicht viel bekannt. 10. Proteinbiosynthese (Translation) Der genetische Code Seine Bedeutung besteht darin, dass er die Nukleotidsequenz der RNA in die Aminosäuresequenz der Proteine zu übersetzen erlaubt. Dabei stehen immer drei Basen (ein sog. Triplett) als Codierung für eine Aminosäure. Allerdings codieren die Tripletts UAA, UGA und UAG nicht für Aminosäuren, sie stellen ein "Stop-Signal" dar (s.u.). Das Triplett AUG codiert Methionin und stellt häufig den Startpunkt für ein neues Protein dar. Man sagt vom genetischen Code sei, - universal: Bei allen Lebewesen gilt die gleiche Codierung für die Aminosäuren. Von dieser Regel gibt es einige seltene Ausnahmen, z.B. stellt die Folge UAC, die normalerweise Tyrosin codiert, bei Pantoffeltierchen ein weiteres Stopsignal dar. - degeneriert, 43.= 64 Basen/20 Aminosäure, d.h. für jede AS codieren mehr als ein Triplett (Ausnahmen sind Trp, Met, für die nur ein Triplett codiert) - konservativ. d.h., die zweite Base entscheidet über den Charakter der einzubauenden AS. So codiert ein A in der zweiten Position des Tripletts fast immer für eine polare AS und ein U immer für eine hydrophobe AS. - kommafrei, keine stummen Nukleotide, keine Lücken, nicht überlappend. Auch hiervon gibt es Ausnahmen. Virale Gene enthalten manchmal auf einem Gen mehrere Startpunkte, die für verschiedene Proteine codieren. - unidirektional, nur in einer Richtung gelesen. Auch hiervon sind Ausnahmen auf viralen Genomen entdeckt worden. Das Hepatitis-B-Virus benutzt sein Genom in beiden Richtungen zur Proteinsynthese. Ribosomen sind aus Proteinen und RNA zusammengesetzt. Wir unterscheiden eine große und eine kleine Untereinheit, die entsprechend ihrer Sedimentation bei Zentrifugationen als 60S und 40S-Untereinheit bezeichnet werden. Die 40 S-Untereinheit enthält 33 Proteine und die 18 S-RNA; die 60 S-Untereinheit enthält 49 Proteine, sowie die 28, 5.8, und 5 S-RNA. Die ribosomalen RNA-Formen enthalten viele Helixregionen mit Basenpaarungen. Sie entstehen aus Primärtranskripten, die auch ein tRNA-Molekül enthalten Für die Proteinsynthese müssen beide Ribosomen-Untereiheiten miteinander verbunden sein. Ribosomen kommen entweder frei im Cytosol vor oder sind am ER gebunden, das man als rauhes ER im Mikroskop sieht. Ribosomen besitzen eine kompakte Struktur mit mehreren Bindungsstellen (mindestens 3): - eine für die mRNA, - eine für die wachsende Peptidkette sowie für die ankommende Aminosäure - eine für die Peptidyltranferase - außerdem Erkennungsstellen für Regulatoren. Aminoacyl-tRNA Zur Aktivierung der Aminosäuren katalysiert die Aminoacyl-tRNA-Synthetase die Bildung eines Aminoacyladenylates über eine Bindung der Carboxylgruppe an AMP (das ist wiederum eine labile, "energiereiche" Säureanhydridbindung), wobei PPi frei wird, dessen Hydrolyse das Gleichgewicht der Reaktion in Richtung Kopplung verschiebt. Dieselbe Aminoacyl-tRNA-Synthetase (zweiköpfiges Enzym) überträgt die so aktivierte AS auf das freie 2'- oder 3'-OH der tRNA und kontrolliert die Korrektheit des Sitzes. Wenn es nicht genau paßt, wird die Bindung wieder hydrolysiert. Das Enzym verfügt über eine sehr hohe Substratspezifität: z. B. muß die Tryptophan-spezifische Aminoacyl-tRNA-Synthetase die AS Tryptophan an die Tryptophan-spezifische tRNA anhängen. Passiert hier ein Fehler wird eine falsche AS in das Protein eingebaut. Die Fehlerrate im Protein ist 1:10000, die der Bildung des Zwischenproduktes 1 : 200. Hieraus wird deutlich, wie effektiv der Korrekturmechanismus arbeitet. Translationsmechanismus Die Initiation erfordert die Assoziation der Ribosomenuntereinheiten. Die mRNA bindet mit einer spezifischen Bindungsstelle an des Robosom, sie enthält das Startcodon AUG (codiert Methionin). Weiterhin enthält der Initionskomplex die Starter-tRNA (Methionyl-tRNAf), GTP und mindestens 6 Initiationsfaktoren ( eIF, eukaryontischer Initiations-Faktor). Die an der Starter-tRNA gebundene Aminosäure Methionin ist formyliert (N10Formyl-FH4). Damit ist die NH2-Gruppe blockiert, wodurch die Richtung der Protein-Synthese festgelegt ist. eIF-2 unterscheidet z.B. zwischen normaler Met-tRNAm und Starter-Methionyl-tRNAf. Diese bindet am Peptidyl-Zentrum auf dem Ribosom. An einer mRNA können mehrere Ribosomen arbeiten (Polysomen). Bei der Elongation wird die nächste, mit der AS beladene tRNA an die dem P-Zentrum benachbarte noch freie Aminoacylbindungsstelle (A-Zentrum) gebunden (Codon-AnticodonWechselwirkung). Hierür ist der Elongationsfaktor eEF-1 und nötig. Die Regenierung des aktiven eEF1 benötigt GTP und den Guaninnucleotid-Austauschfaktor eEF1. Die Transpeptidase katalysiert die Knüpfung der Peptidbindung zwischen der NH2-Gruppe der im A-Zentrum sitzenden Aminoacyl-tRNA und der COOH-Gruppe der im P-Zentrum gebundenen Formyl-Methionyl-tRNAf. Das erfolgt spontan, weil die Esterbindung zwischen der AS und der tRNA eine hohe Hydrolyseenthalpie von -29 kJ besitzt und deshalb kein zusätzliches energiereiches Phosphat mehr nötig ist. Die nun nicht mehr beladene Methioninspezifische tRNAf dissoziiert ab. Anschließend erfolgt die Translokation der Peptidyl-tRNA (mit der mRNA) aus dem A-Zentrum in das P-Zentrum mit Hilfe von eEF2. Die Termination geschieht beim Erreichen eines Stopcodons ( S15). Die Peptidkette wird auf Wasser übertragen, und ein Releasingfaktor setzt das Protein frei (eRF), was auch wieder GTP-abhängig ist. Hemmstoffe der Translation; ADP-Ribosylierung (Inaktivierung) von eEF2 durch Diphtherietoxin Regulation der Translation: Am besten ist die Aktivierung des eIF-2 untersucht, der im phosphorylierten Zustand inaktiv ist und erst durch eine Proteinphosphatase wieder aktiv wird. Z.B. aktivieren die Interferone diesen Faktor, und Häm inaktiviert ihn, was die Hemmung der Synthese viraler Proteine bei viralen Infektionen und die Aktivierung der Globinsynthese bei Häm-Überschuß erklärt. 11. Die Proteinfaltung Unmittelbar nach dem Austritt aus dem Ribosom falten sich die Sekundärstrukturen, ohne daß sie jedoch die gegenseitigen Positionen korrekt einnehmen (molten globule, geschmolzenes Knäuel). Die Aminosäuresequenz eines Polypeptides enthält alle Informationen, die benötigt werden, um die Kette in die native, dreidimensionale Struktur zu falten. (vergl. partieller Doppelbindungscharakter der Peptidbindung). Beispiel: Denaturierung/Renaturierung von Ribonuklease. Durch Harnstoff und einen Überschuss an Reduktionsmittel wird das Enzym Ribonuklease A denaturiert und seine Disulfidbrücken gesprengt. Danach erfolgt die Renaturierung durch Entfernen des Harnstoffs durch Dialyse, Zusatz von geringen Mengen Reduktionsmittel (-SH) beschleunigt den Renaturierungsprozess und die erneute Ausbildung von Disulfidbrücken. Aber: Die Ausbildung der nativen Struktur durch spontane Ausbildung/Überprüfung möglicher Konformationen nach dem Versuch/Irrtum-Prinzip ist ein extrem langsamer Prozeß (LEVINTHAL-Paradoxon). Faltungshilfen: 1. Proteindisulfidisomerasen (PDI) Setzt man die PDI zu, erfolgt der Rückfaltungsprozess denaturierter Ribonuclease sehr viel rascher. 2. Faltungsenzyme: Prolin-cis-trans-Isomerasen Im Prolin ist die für die Peptidbindung notwendige NH-Gruppe im Ring sterisch fixiert und nicht wie bei den anderen AS frei beweglich. Damit sind zwei unterschiedliche Richtungen möglich, in der die Polypeptidkette sich nach einem Prolinrest fortsetzt, die thermodynamisch wahrscheinlichere ist die trans-Konfiguration. Ca.10 % der Peptidbindungen in Proteinen sind jedoch Prolin-cis-Bindungen. Durch die Prolin-cis-trans-Isomerasen werden in der fertigen Peptidkette Prolin-trans-Bindungen zu Prolin-cis-Bindungen isomerisiert. 3. Chaperone Chaperone binden cotranslational an die wachsende Polypeptidkette. Sie verhindern Kollabieren, Aggregation, Wechselwirkungen von Domänen des noch nicht fertig gestellten Proteins, Wechselwirkung mit anderen Proteinen. Sie verhindern dadurch falsche Faltung bzw. fördern die Rückfaltung denaturierter Proteine. Sie werden unter Stress-Situationen besonders vielfältig gebildet, weil in diesem Fall sowohl falsche Faltungen auftreten, die korrigiert werden müssen, als auch die Proteinsynthese angeschaltet wird ( S13). Erstmalig wurden die Chaperone beschrieben, als Hefe-Zellen dem Stress der Hitzeeinwirkung (bei Hefen ist eine Erhöhung der Kultivierungstempartur auf 40 °C bereits ein "Hitze-Schock") ausgesetzt wurden, weshalb diese Proteine auch Hitzeschock-Proteine genannt werden (hsp 60, 70, 90). Chaperone kommen in allen Organismen vor. Beispiele: 1. Hsp 70: DnaK/DnaJ 2. GroEL/ES (bakteriell). Es ist tonnenförmig aufgebaut. Das frisch synthetisierte Protein wird durch die Höhlung quasi hindurch massiert, wobei die hydrophilen Bereiche nach außen und die hydrophoben nach innen gedrängt werden. Bei einem Durchtritt durch das Molekül werden 7 Moleküle ATP verbraucht, was zeigt, dass die Zellen viel Energie aufwenden, um die Proteine richtig zu falten. Solche Passagen durch das GroEL können mehrfach hintereinander erfolgen, bis die korrekte Konformation erreicht ist und dem Protein der Eintritt in das GroEL-Molekül nicht mehr gelingt. Amyloidogenese Prion-Protein (PrPC): Glykoprotein, normaler Zellmembranbestandteil von Gehirnzellen, Funktion unklar 254 Aminosäuren; 4 -Helices; Pathologische Isoformen (Konformations-Isomere) des Prion-Proteins: PrPCJD (CREUTZFELD-JAKOB-Disease): PrPSc (Scrapie); 2 -Helices, 4 -Faltblattstrukturen -Faltblätter von PrPSc bindet an PrPC und erzwingen Umfaltung von PrPC PrPSc. PrPSc = schwer wasserlöslich, säurestabil, hitzestabil, resistent gegenüber Proteasen, aggregiert Abblagerung von Aggregaten im Gerhin von CREUTZFELD-JAKOBPatienten: 4 Formen: 1. familiär (genetisch) bedingt 2. iatrogene/erworbene Form 3. sporadische Form 4. vCJD durch Aufnahme von BSE-Rinder-Produkten Test: Proteaseverdau, PrPSc resistent, PrPC abbaubar Elektrophorese(WESTERN-Blot). 12. Post- und cotranslationale Modifikation der Proteine 1. Limitierte Proteolyse Sie dient der Aktivierung der Proteine oder der Generierung kleiner biologisch aktiver Moleküle. Beispiele: Angiotensin I und II Hormone: Vasopressin; Proopiomelanocortin (POMC), das aus 265 AS besteht und aus dem sowohl ACTH, -MSH, CLIP und -LPH sowie die Endorphine -MSH und METEnkephalin entstehen können; Proinsulin/Insulin; Enzyme der Gerinnungskaskade und des Komplementsystem; Pepsinogen, Trypsinogen und alle Proteasen. 2. Glykosylierung ist neben der limitierten Proteolyse die häufigste Modifikation. Man findet sie bei Eukaryoten, Viren und Archebakterien, kaum jedoch bei Bakterien (außer bei der Synthese des Mureins der GRAM-positiven Bakterien). Die Kohlenhydratreste sind entweder O-glykosidisch (auf Ser- und Thr-Hydroxyle) oder N-glykosidisch (auf Asn in der Sequenz Asn-X-Ser/Thr) gebunden. Sie werden im ER aufgebaut, auf das Protein übertragen und im ER und im GOLGIApparat getrimmt, d.h. zurechtgeschnitten ( S20). Die am häufigsten gefundenen Monosaccharide sind Man, Gal, Fuc und GlucNAc. Sie üben vielfältige Funktionen aus, vor allem in membranständigen (Glykokalix) und sezernierten Proteinen (Serumproteine außer Albumin). Sie sind für die Individualität verantwortlich (Blutgruppensubstanzen), bilden die extrazelluläre Matrix mit in Form der Proteoglykane, einige Hormone sind glykosyliert. Selten sind die KH-Reste an der biologischen Wirkung beteiligt. 3. Hydroxylierung findet extrazellulär an den AS Prolin und Lysin bei der Kollagenreifung statt. Die Hydroxylierung führt zur Ausbildung zusätzlicher H-Brücken. Die Hydroxylierung ist eine Oxidation, die Askorbinsäure (Vitamin C)-abhängig ist. Vitamin C ist Coenzym von Oxidoreduktasen, das bei Hydroxylierungsreaktionen z.B. bei der Kollagen-Synthese und der Synthese von Nebennierenhormonen erforderlich ist. Bei Vitamin C-Mangel kann die Reifung des Kollagens nicht mehr richtig stattfinden, Mangel-Syndrom Skorbut. 4. Phosphorylierung durch Proteinkinasen findet in Proteinen an Tyrosin-, Serin- und Threonin-Hydroxylen statt. Es ist die häufigste Art der reversiblen Aktivierung und Inaktivierung von Proteinen, von und auch als Element der. Beispiel: Enzyme des Intermediärstoffwechsels; Signalvermittlung von Hormon- und Wachstumsfaktor-Rezeptoren (Zellzyklus: Cyclin-abhängige Kinasen ( S6); Eine moderne, sich rasch entwickelnde Therapieform ist die sog. Signaltransduktionstherapie, die in diesen reversiblen Regulationsmechanismus eingreift, indem sie die Kinasen und Phosphatasen hemmt. 5. Farnesylierung, Myristinylierung (C-14) und GPI-Anker viele Membranproteine sind durch Anfheftung von Farnesylsäure bzw. Mristinsäure (C14) in den Lipiddoppelschichten fixiert. Glykosyl-Phosphatidyl-Inositol-Anker enthalten an den Inositolresten noch Monosaccharide gebunden. Auch diese Modifizierung findet im ER statt, d.h. also unmittelbar nach der Protein-Synthese. 6. Acetylierung schützt am N-terminalen Ende vor dem Abbau durch Exopeptidasen, die im Cytosol in hoher Aktivität vorkommen. Acetylierung von Histonen, Transkription ( S4). Diese Modifizierung ist als Pendant zur prokaryontischen Formylierung von Methionin zu sehen. 7. Carboxylierung von Glutamat in den Gerinnungsenzymen ist eine spezifische Modifikation. Sie findet in der Leber statt und ist abhängig vom Vitamin K, einem fettlöslichen Vitamin. Durch die Carboxylierung erhält das Glu eine weitere negative Ladung am -C-Atom, durch das Ca++-Ionen gebunden werden können, die für die Wirkung der Gerinnungsenzyme essentiell sind. Antagonisten des Vitamin K werden prophylaktisch als Gerinnungshemmer bei Patienten mit erhöhtem Infarktrisiko eingesetzt. 8. Vervollständigung von manchen Enzymen und Funktionsproteinen wie Hb und Cytochrome, Katalase, Xanthinoxydase durch die Einlagerung von Metallionen. 9. Protein-Spleißen Autokatalytisches Ausschneiden eines Peptides aus der Mitte eines Proteins (Intein). Verknüpfung der dadurch entstehenden N-terminalen und C-terminalen Peptide (Exteine) durch intramolekularen Peptidyltransfer unter Ausbildung eines Thioester-Intermediates. 13. Intrazellulärer Transport von Proteinen Wege für den Proteintransport: - Transport durch Poren (die selektiv sein können) - Transport durch Membranen (benötigen Translokatoren) - Transport über Vesikel (durch Abschnüren und Verschmelzen) Transport durch die Kernmembran: Die Kernporenkomplexe bestehen aus ca. 100 Proteinen und haben eine Größe von 125 000 kD. Ein Kern hat 3 000 - 4000 Poren, was von der Transkriptionsaktivität abhängt. Kernproteine werden im Cytosol von freien Ribosomen synthetisiert. Wasserlösliche Moleküle mit weniger als 5 kD können frei passieren. Das kritische MW, das offenbar nicht mehr passieren kann, liegt bei 60 kD, der Kanal ist 9 nm im Durchmesser und 15 nm lang. Größere Proteine wie die aggregierten ribosomalen Proteinkomplexe werden aktiv transportiert Proteintransport: Cytosol Kern Die Proteine (Fracht) binden dabei über die Lys-Reste (Kernlokalisationsignalsequenz: ProLys-Lys-Lys-Arg-Lys-Val) an das cytosolische Transportprotein Importin. Nach Bindung von Importin dockt der ternäre Komplex an die Kernpore an und wird unter Vermittlung und Kontrolle des RanGDP-Proteins durch die Pore geschleust. Durch Bindung eines RanGTPProteins im Kern an Importin wird der trimere Komplex gespalten und das Fracht-Protein frei. Proteintransport: Kern Cytosol Die Frachptoteine werden durch Bindung an Transportproteine Exportin, Karyopherin, Transportin gebunden und unter Beteiligung von RanGTP aus dem Kern transportiert. Protein-Import in das ER (Signalhypothese) erfolgt cotranslational. Ein SRP (vom engl.: signal recognition particle) bindet an das hydrophobe Signal des neu synthetisierten Proteins und inseriert es an den Rezeptor (SRP-Rezeptor) im ER. Da das ganze noch am Ribosom hängt, entstehen so die Polysomen. Es besteht ein wäßriger Kanal unterhalb des SRP-Rezeptors, der in Abwesenheit des Ribosoms verschlossen ist. Das N-terminale Signal verbleibt an der Pore und wird erst von der Signalpeptidase abgeschnitten, wenn das C-terminale Ende im ER ist. Hydrophobe Signalsequenzen im Inneren eines Proteins (Transfer-Stop-Signal) dienen als Transmembrandomänen zum Verbleib der Proteine in Membranen. Die Orientierung solcher Proteine in der Membran ist für immer festgeschrieben. Cotranslational erfolgt im ER die Glykosylierung der Proteine, anschließend findet eine Modifizierung der auf das Protein übertragenen, verzweigten Olisaccharidkette statt (Trimmen: Entfernen von Sacchariden: Glucose, Mannose) Durch Ausknospung von ER-Membranen entstehen Vesikel, in denen sich ER-Inhalt (+ Protein) befindet. Die abgeschnürten Vesikel gelangen zum GOLGI-Apparat und fusionieren mit der Membran der GOLGI-Holräume (cis-Zisterne), damit ergießt sich der Vesikelinhalt in den Zisterneninhalt. Dort setzt sich das Trimmen der KH-Kette fort; durch Vesikeltransport gelangen die Proteine in die medianenen- und trans-Zisternen, in denen sich die Modifizierung der KH-Kette durch aufeinander folgende Anlagerung von Monosacchariden (Fucose, N-Acetylglucosamin, Galactose, Sialinsäure) fortsetzt. Dadurch entstehen die Signale für den Transport im verschiedene Zellkomarptimente bzw. für die Sekretion. Proteine, bei denen die Phosphorylierung der Mannose der KH-Ketten stattfindet, binden in den trans-Zisternen an ein Mannose-6-Phosphat-Rezeptor-Protein, wodurch sie in die Lysosomen dirigiert werden. Wenn diese Markierung ausfällt, kommt es zu einer lysosomalen Speicherkrankheit, der sog. I-cell-disease. Durch Knospung können "leere" Rezeptorproteine wieder zurück zur Membran transportiert werden (Rezeptor-Recycling). ER-residente Proteine enthalten die KDEL (Lys-Arg-Glu-Leu)-Sequenz, durch die sie mit Hilfe eines entsprechenden Rezeptors durch Vesikeltransport aus dem GOLGI-Apparat wieder ins ER zurücktransportiert werden. Der endozytische und der sekretorische Weg sind miteinender verbunden. Das Transportprinzip ist der vesikuläre Transport. Lysosomen können fusionieren mit Endosomen (von der Endocytose), mit Autophagosomen und mit Phagosomen. Ein weiterer Weg des vesikulären Transportes ist die Exocytose. Protein-Import in die Mitochondrien ist besonders erschwert durch die mitochondriale Doppelmembran. Nur wenige mitochondriale Proteine werden von der inneren Membran der M. selbst synthetisiert, und diese müssen oft noch mit den cytosolisch generierten assemblieren. Das erste ist die Bindung an den Rezeptor an der äußeren Membran, der das Signal erkennt. Diese Signale sind auf den Proteinen nicht mehr nachweisbar, wenn die Proteine das M. erreicht haben. Sie werden demnach abgebaut. Die Proteine werden im gefalteten Zustand transloziert, d.h. sie werden sowohl im Cytosol als auch im Mitochondrium von einem (jeweils verschiedenen) hsp 70 gebunden gehalten. Die Translokation erfolgt an definierten Kontaktstellen. Der Prozess benötigt ATP-Hydrolyse. Außerdem wird die elektronenmotorische Kraft der Mitochondrien benötigt, um die Matrixproteine nach innen zu ziehen. 14. Zelluläre Proteolyse Prinzip der Proteolyse ist die hydrolytische Spaltung einer Peptidbindung, die Enzyme werden deshalb auch als Peptidasen oder Peptidhydrolasen bezeichnet, häufig auch als Proteasen oder Proteinasen, wenn sie intakte Proteine angreifen können.. Die Spezifität einer Peptidase ist durch die Aminosäuren definiert, die die zu spaltende Peptidbindung flankieren. Einteilungsprinzipien: 1. Katalysemechanismus: Serin-, Aspartat-, Cystein-, Threonin-, Metalloproteasen, 2. Wirkung: Endopeptidase: spalten in der Mitte eines Proteins, Exopeptidasen: spalten am N-terminalen (Aminopeptidasen, Dipeptidylpeptidasen) oder Am C-terminalen Ende (Carboxypeptidasen, Peptidyldipeptidasen). Peptidasen sind wahrscheinlich die am weitesten verbreitete Enzymklasse. Man findet sie in allen Organismen und allen Organellen. Selbst Viren verfügen in der Regel mindestens über eine eigene Peptidase. limitierte Proteolyse: ( S18) gezielten Aktivierung oder Inaktivierung aktiver Proteine totale Proteolyse: (Protein-Verdauung) komplette Beseitigung falscher oder nicht mehr benötigter Proteine sowie der Bereitstellung von AS für die Proteinsynthese. Proteolytische Enzyme sind oft in Kaskaden angeordnet. Die intrazelluläre Proteolyse ist für den dynamischen Zustand der Proteine verantwortlich, alle Proteine unterliegen einem Umsatz. Die Halblebenszeiten verschiedener Proteine liegen zwischen wenigen Minuten (Enzyme des Aminosäurestoffwechsels) und vielen Monaten (Kollagen). Beispiele mit großer biologischer Bedeutung Das cytosolische Proteasom hat die Aufgabe, falsch gefaltete Proteine oder auch gealterte Enzyme zu eliminieren. Solche Proteine werden an Ubiquitin gekoppelt, ein 76 AS langes, überall vorkommendes Protein. Diese Markierung dirigiert das abzubauende Protein zum Proteasom. Das Proteasom besteht aus vier ringförmig angeordneten Moleküllagen, deren jedes aus sieben Proteinen besteht. Es sedimentiert mit 20 S und bildet eine Art Fass, in das das abzubauende Protein wahrscheinlich durch das Ubiquitin hineingezogen wird. Im Inneren der fassförmigen Struktur befinden sich die Threoninreste, die das aktive Zentrum bilden, und die Proteine in ca. 7 AS lange Peptidfragmente zerlegen. Der Abbauweg ist fein reguliert und kann auch ganz schnell reagieren, z. B. ist der cyclische Abbau der Cycline Proteasomkatalysiert. Das Proteasom ist hoch konserviert in der Evolution. Es findet sich schon bei Archae. Das Proteasom ist auch für die Prozessierung von Antigenen verantwortlich, die über die MHC Klasse I Moleküle präsentiert werden. Die Caspasen vermitteln die Apoptose, in dem sie diese entweder in Gang setzen oder durchführen. Caspasen sind aus zwei nicht identischen Untereinheiten zusammengesetzt, werden als inaktive Vorstufen synthetisiert und durch einen der bereits behandelten Auslösemechanismen aktiviert. Mehrere Caspasen (es sind bis jetzt 12 beschrieben) bilden eine Kaskade von Ereignissen, die damit endet, dass eine Exekutierungsphase die relevanten Proteine in der Zelle hydrolysiert, was dann letzten Endes zu den einzelnen Ereignissen führt, die die Apoptose charakterisieren, z. B. dem Abbau eines DNAse-Inhibitors. Lysosomale Proteinasen (Cathepsine) katalysieren in der Regel eine Totalhydrolyse. Es gibt mindestens 10 verschiedene Cathepsine, sie kommen meist in allen Lysosomen vor, können jedoch auch gewebespezifisch lokalisert sein. Dies trifft z.B. für das Cathepsin K zu, das fast ausschließlich in den Lysosomen der Osteoklasten vorkommt und den Kollagenabbau katalysiert. Eine Mutation im aktiven Zentrum des Cathepsin K führt zum Krankheitsbild der Pyknodysostosis, an der der frz. Maler Toulouse-Lautrec litt und die durch Knochenbrüchigkeit und schlechte Heilungstendenz gekennzeichnet ist, die Ursache der Kleinheit von T.-L. 15. Biochemie der Viren Viren sind hochmolekulare Partikel, die aus DNA oder RNA und Proteinen bestehen. Sie sind Krankheitserreger (z. B. Mumps, Röteln, Schnupfen, AIDS, Hepatitis, Pocken, Krebs). Viren kommen intrazellulär und extrazellulär (Virionen) vor. Viren können sich selbst nicht vermehren, sie sind auf den Proteinsyntheseapparat von Wirtszellen angewiesen. Virus-Typen Sie bestehen aus der Nukleinsäure und dem symmetrisch angeordneten Capsid, das aus mehreren Capsomeren besteht. Während die NS die genetische Information trägt, schützt das Capsid das Virus vor Abbau und determiniert dessen Antigenität. Eindringen: Die Virushülle vermittelt das Eindringen in die Wirtszelle. Viren benutzen zelleigene Rezeptoren zum Eindringen in die Wirtszelle, wobei sie ihre eigene strukturelle Ähnlichkeit mit den natürlichen Liganden ausnutzen. Dadurch kommt die Gewebs- bzw. Zellspezifität zustande, wie z.B. beim HIV die Bindung an T-Zellen über das CD-4 Molekül erfolgt. (Cytomegalievirus2-Makro-globulin der Zellmembran, EPSTEIN-BARRVirusKomplement-Rezeptor CR2, Adenoviren (HTLV-1, SV40)MHC-I-Molekül, TollwutvirusAcetylcholin-Rezeptor, Reoviren-adrenerger Rezeptor, MKS-Virus Integrine Vermehrung der Viren: permissiv (lytisch) oder nicht permissiv (Transformation) Das genetische Material der Viren kann sowohl RNA als auch DNA sein, demzufolge unterscheiden wir RNA- und DNA-Viren. RNA-Viren können außerdem noch in doppel- und einzelsträngige und letztere wieder in solche mit negativer und positiver (kann direkt wie mRNA translatiert werden) Polarität eingeteilt werden. Retroviren besitzen das Enzym reverse Transkriptase, die die RNA in cDNA umschreibt. Eine Integrase bewirkt, daß die cDNA in das Wirtsgenom integriert wird. Typ 1: (Poliovirus) enthält (+)RNA, sie wird zu (-)RNA repliziert, mit der (+)mRNA synthetisiert wird (RNA-abhängige RNA-Polymerase). Typ 2: (Influenza-, Tollwut-, Ebola-, Marburg-Viren) eenthält (-)RNA, die direkt der (+)mRNA-Synthese dient (RNA-abhängige RNA-Polymerase). Typ 3: (Reoviren) enthält doppelsträngige (+)RNA/(-)RNA, an deren (-)RNA, die (+)mRNA synthetisiert wird (RNA-abhängige RNA-Polymerase). Typ 4: (Retroviren) enthält (+)RNA). Durch RNA-abhängige DNA-Polyerase wird (-)DNA gebildet, Wirts-tRNA dient als Primer, daran wird (+)DNA (+)DNA/(-)DNA. Am (–)DNA-Strang wird die (+)mRNA synthetisiert HIV-Virus: enthält - 2 identische Stränge von (+)RNA (9.7 kb) - RNA-abhängige DNA-Polymerase (Revertase) - Gerüstproteine gp18, gp24 - transmembranes Glykoprotein gp 41 in der Lipiddoppelschicht Glykoprotein gp 120 hängt gebunden an dem gp 41 (das als Ankerpotein wirkt). Es ragt aus dem Virus heraus, wird vom Immunsystem des AIDS-Infizierten als fremd erkannt, der dagegen Antikörper bildet. Diese können durch Western-Blot nachgewiesen werden. - Integrase: katalysiert die Integration der Virus-DNA nach reverser Transkription der VirusRNA in die DNA (Genom) des Wirts - Protease: spaltet aus den Polyproteinen die o.g. Proteine Die Polyproteine werden durch drei Virus-DNA-Gene codiert 1. GAG-Gen (gruppenspezifisches Antigen): gp 18, gp24 2. POL-Gen (Polymerase): Revertase, Integrase, Protease 3. ENV-Gen (Envelope): Hüllproteine gp41, gp120 Infektion: HIV-1 =lymphotropes Virus: befällt T4-Lymphocyten (T4-Zellen sind unverzichtbarer Bestandteil des Abwehr-Systems, sie binden mit dem T-Zell-Rezeptor und einem CD4-Bindungsprotein an das MHCII-Molekül von Antigen-präsentieren-den Zellen (Makrophagen). Daraufhin bilden die T4-Zellen Lymphokine (Interleukin 2), das B-Lymphocyten zur Immunantwort (Antikörperbildung) stimuliert.) Das HIV-1-Virus bindet mit dem Hüllprotein gp120 an das CD4-Molekül. Konformationsänderung im CD4-GP120-gp41-Komplex. Senkung der Affinität von gp120 zu gp41, Steigerung der Affinität des gp120CD4-Komplexes zum T4-Zell-Co-Rezeptor CCR5 Ablösung des Hüllproteins gp120 von seinem Ankerprotein gp41 Bindung des HIV-1-Virus mit dem gp41-Protein an die T4-Zellmembran lokale Destabilisierung der Membran, Fusionspore, Fusion von Virusmembran mit Zellmembran Internalisierung des Capsids, Freisetzung der Virus-RNA Reverse Transkription der Virus-RNA RNA-DNA-Hybrid, Umschreibung in doppelsträngige DNA Integration der Virus-DNA in das Wirtsgenom (Integrase) Synthese von Virus, RNA, Virus-Proteinen, HüllproteinenEinbau in Plasmamembran Freisetzung der Viren durch Abknospung (budding). Für die Infektion sind neben dem CD4-Molekül der Co-Rezeptor CCR5 (= Chemokin-bindender Rezeptor) erforderlich. Diese wurden auch als "AIDS-Resistenzgene", weil Menschen, die eine Mutation in dem Corezeptor aufwiesen, nicht an AIDS erkrankten. Die HIV-befallenen T4-Lymphocyten sterben nach Monaten ab, Virsureservoir sind dann die Makrophagen. Im Verlauf der Erkrankung sinkt die Anzahl der T4-Lymphocyten drastisch ab, die Patienten sterben an Erkrankungen der Immundefizienz. HIV-Revertase hat hohe Fehlerrate (10 x höher als bei Reoviren), Polymerase fehlt Reparaturaktivität deshalb hohe Variabilität der HIV-Virus-Proteine schwierige Impfstoffherstellung. Therapie: 1. Aciclovir, Ganciclovir und Azidothymidin nutzen entweder die Tatsache aus, daß virale Enzyme (Thymidinkinase) diese Substanzen phosphorylieren und als "Bausteine" für die Nukleinsäuren in infizierten Zellen einsetzen oder daß die Transkriptionsrate in infizierten Zellen besonders hoch ist und dadurch der Einbau von solchen "kettenbrechendenen" Bausteinen wahrscheinlicher ist als in nicht infizierten Zellen. Wegen der Resistenzentwicklung gegen diese Hemmstoffe (die HI-Viren tauschen die Codons für die betreffenden Aminosäuren in der Revertase aus!) werden die Nucleosidanaloga in Kombination verabreicht 2. Hemmstofer der HIV-Protease durch substratanaloge, nicht metabolisierbare Inhibitoren 3. Versuche: Antikörperentwicklung, Förderung der zellulären Abwehr, Beeinflussung der Chemokinbindenden Rezeptoren HBV (Hepatitis B-Virus) ist ein DNA-Virus, sehr klein, enthält eine Proteindomäne in der Hülle, die aus 226 AS besteht. Nur 3200 Nukleotide lang, der Plusstrang ist um 20 - 50 % kürzer als der Minusstrang. Das HBV-Genom hat nur vier Gene, zeigt aber Verschiebungen des Leserasters und hat cis verstärkende Elemente. Der auf den Hepatocyten erkannte Rezeptor ist noch nicht identifiziert, vielleicht ist es der IL 6-Rezeptor. HBV bildet eine RNA als Zwischenstufe, wobei die Matrizen-DNA persistiert aber nicht in das Genom der Wirtszelle integriert wird, weil die Integrase fehlt. HBV Antigene werden offenbar nicht von den TZellen erkannt, deshalb entgeht das HBV dem Immunsystem. Die Prä-genomische RNA wird dann mit einer reversen Transkriptase in die virale DNA umgeschrieben und die Matrizen RNA mittels der RNAse-Domäne der Polymerase abgebaut. HBV mutiert häufiger als andere DNA-Viren wegen der mit beteiligten reversen Transkriptase. Ein Gly-Arg-Austausch wird als Fluchtmutante bezeichnet, weil sie der Immunabwehr entgehen kann. Das Virus ist nicht zytopathisch, sondern die chronische Hepatitis B ist ein durch immunologische Prozesse in Gang gehaltenes Krankheitsbild. Es kann zum hepatozellulären Krebs entarten. Dann findet man immer Virus DNA-Sequenzen in das Genom der Wirtszelle integriert. Der Zusammenhang zwischen Virusinfektion und maligner Entartung ist bisher nicht aufgeklärt. 16. Cancerogenese Krebszellen: - wachsen autonom (unkontrolliert), keine Kontakthemmung - invadieren ins umliegendes Gewebe, - erzeugen Tochterabsiedlungen (Metastasen) Ausschwemmung von Zellen aus dem Primärtumor und Ansiedelung in anderen Geweben - stammen in der Regel von einer einzigen Zelle ab, die mutiert ist (klonale Expansion). In deren Nachkommen spielen sich weitere Mutationen ab (Umprogrammierung der Genexpression, genomische Instabilität). - sind im Vergleich zur Ursprungszelle entdifferenziert. - exprimieren auf ihrer Oberfläche Tumorantigene, die es auf normalen Zellen nicht gibt. - exprimieren Angiogenesefaktoren und Adhäsionsmoleküle, wodurch sie sich über selbst ge-bildete Blutgefäße mit Sauerstoff und Nährstoffen versehen und an Gefäßwänden anhaften können. - haben verändertes Stoffwechselprofil: hohe aerobe Glykolyse; gesteigerte Substrataufnahme (AS, Glucose); veränderte Enzymausstattung im Energiestoffwechsel, Proteinsynthese; Sekretion proteolytischer Enzyme als Voraussetzung für infiltratives Wachstum. Entstehung von Krebszellen 1. Viren (tumorauslösende Retroviren: Onkornaviren) Da die meisten normalen Zellen sich in der Go-Phase befinden, sich also nicht teilen, Krebszellen dies aber ungehindert tun, müssen Möglichkeiten existieren, die Zellen aus der Go-Phase heraus zu bringen. Eine wichtige Entdeckung der modernen Genetik war es, Gene gefunden zu haben, die für diesen Vorgang verantwortlich sind. Der kritische Punkt im Zellzyklus ist das Durchlaufen des Startpunktes, von dem aus kein Weg zurück mehr möglich ist ( S5). Es gibt den Zellzyklus-aktivierende und -hemmende Genprodukte. Manche Mutationen in maligne entarteten Zellen führen in den aktivierenden Genabschnitten zur Hyperaktivierung, in den hemmenden zu einer Unterbrechung der Hemmwirkung. Man unterscheidet deshalb Mutationen in Proto-Onkogene (die dabei zu Onkogenen, krebsauslösenden Genen werden) und in Tumorsupressorgenen (vgl. p 53- Gen im Kapitel Zellzyklus). Krebs kann deshalb als eine genetische Erkrankung angesehen werden. Viren haben bei der Entdeckung der proto-Onkogene eine große Rolle gespielt, obwohl sie für die Krebsentstehung beim Menschen wohl keine große Rolle spielen. PEYTON ROUS entdeckte das erste Tumorvirus um 1910, ein Retrovirus, das bei Hühnern ein Sarkom (Bindegewebskrebs) hervorruft. Wenn Zellen in einer Kultur mit dem Virus infiziert werden, zeigen sie Zeichen der malignen Transformation: sie werden beweglich, zeigen nicht mehr das Phänomen der Kontakt-hemmung, werden unsterblich und proliferieren in Abwesenheit von Wachstumsfaktoren. Wenn man sie in Tiere zurücktransplantiert, entstehen Tumoren. Die wichtigste neue Entdeckung war, daß das Virus nicht mehr transformierte, wenn in einem viralen Gen eine Mutation auftrat, die zwar für das Virus völlig bedeutungslos, aber für die Krebserzeugung essentiell war. Es handelt sich um das v-src-Gen, das im Genom vieler Tiere eine Entsprechung hat, das cytosolische c-src-Gen, das gegenüber dem viralen geringfügig verändert ist. Das v-src-Gen ist von einem Retrovirus bei einer früheren zellulären Passage aus dem Genom aufgenommen und im Laufe der Virusreplikation oft mutiert worden. Man kann solche viralen Onkogene durch Hybridisieren mit zellulärer DNA auffinden und damit auch die zellulären Proto-Onkogene identifizieren. Das cytosolische c-src-Gen codiert normalerweise für eine Proteinkinase, die in der intrazellulä-ren Signalweiterleitung bei der Regulation des Wachstums und der Proliferation von Zellen be-teiligt ist. Das Produkt des v-src-Gens ist nicht mehr regulierbar und führt deshalb in den befallenen Zellen zu einer Daueraktivierung, d.h. Dauerproliferation, also genau das, was die maligne Transformation ausmacht. Auch mutierte TumorsupressorgenProdukte können eine cancerogene Wirkung auslösen. Die Papillomvirusprodukte E6 und E7 hemmen die Wirkung von p 53 und Rb ( S6) und erhöhen damit die Mutationsrate in den infizierten Zellen, die wiederum als Konsequenz die Entstehung eines Tumors haben können. 2. Ionisierende Strahlung 3. Cancerogene Benzpyren, Aflatoxin, 3-Methylcholanthren, Diethylstilbestradiol (synthetisches Östrogen), Buttergelb, Asbest, Benzol, Benzidin, Nitrosamine Cancerostatika 1. Hemmung der Nukleotid-Synthese Aminopterin, Amethopterin (Methotrexat) = Folsäureantagonisten: hemmen die Dihydrofolat-Reduktase Fluoruraciul = Hemmstoffe der Thymidylatsynthase Azoserin = Glutaminanaloga, hemmen die Glutamin-Amidotransferasen (wichtige Reaktion bei Basensynthese 6-Mercaptopurin wird zu Mercaptoribonucleotid = hemmt Bergungsstoffwechsel (HGPRT 2. Hemmung der DNA-Synthese Cytosinarabinosid (Ribose ist durch Arabinose) hemmt als CTP-Analogon die DNA-Polymerasen Acyclovir, Ganciclovir = Guaninanaloga; werden in die DNA-eingebaut und hemmen Elongation, Einsatz auch als Virostica 3. alkylierend wirkende Cytostatika Gelbkreuz, Stickstofflost, Cyclophosphamid, Äthylenimin verknüpfen die DNA-Stränge kovalent = Hemmung der Polymerasen Cisplatin = vernetzend (nicht alkylierend) wirkendes Cytostatikum 4. Angiogenese-Hemmer Endostatin 17. Gentherapie Gentherapie heißt Therapie mit genetischem Material. Es ist im Moment ein reines Forschungsgebiet. Fehler im Genom einer Einzelzelle in vivo gezielt zu korrigieren, ist heute nicht möglich. Manipulationen und damit auch Korrekturen in frühen Stadien der Embryonalentwicklung ex oder in vivo sind in Europa zur Zeit gesetzlich verboten (in Deutschland regelt das das Embryonenschutzgesetz). Die Vielzahl der Zellen im Körper (rund 1014 bis 1015) und die große Zahl der Nukleotidpaare im Genom, dazu dessen kompakte Verpackung machen den direkten Ersatz eines mutierten Gens im gesamten Körper unmöglich. Folgende Gentherapieansätze sind heute möglich: - Ersatz der Leistung eines defekten Gens (Versuche bei Mukoviszidose, Adenosindesaminasemangel befinden sind in klinischen Studien) - Expression therapeutischer Genprodukte (IL-2, Insulin) - Sensibilisierung von Tumorzellen gegenüber radiologischer oder pharmakologischer Intervention (strahleninduzierbare Promotoren für TNF , pro-drug Aktivierung) - Erhöhung der Immunogenität von Tumorzellen (Kopplung tumorspezifischer AK mit Superantigenen zur Auslösung der T-Zell-Antwort) - Einsatz von Antisense-RNA ( S12), um die Translation von Onkogenprodukten zu verhindern. Wichtigste zu lösende Probleme: - Auffinden der mutierten Gene, die für eine Erkrankung verantwortlich sind. Erreichen der Zielzellen, Vektorentwicklung ( S10). Besonder gut geeignet erscheinen Adenoviren zu sein, denen man EF1 ( S16) entfernt hat und damit die Replikationsfähigkeit genommen hat. - Stabilität der transfizierten DNA/RNA in der Zielzelle - Etablierung von geeigneten Tiermodellen und Verifizierung des Effektes im Tiermodell - Sicherheit für Patient, Arzt und Umwelt (z.B. darf die zu transferierende DNA keine Antigenität besitzen, sonst würden sich Autoimmunerkrankungen entwickeln) - Akzeptanz in der Bevölkerung