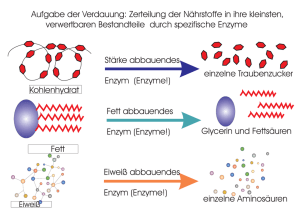
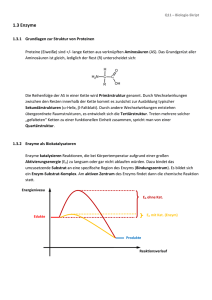
Das aktive Zentrum von Enzymen
Werbung

Entropie ist ein Maß für den Ordnungszustand eines thermodynamischen Systems (chem. Reaktion in einem geschlossenen System); kann auch als Maß für die Nichtumkehrbarkeit (Irreversibilität) eines Vorganges bezeichnet werden Bsp. : je mehr die Moleküle zweier Gase miteinander vermischt sind, desto geringer ist die Wahrscheinlichkeit, dass sie sich wieder entmischen; Je stärker sie gemischt sind, desto mehr Energie muss aufgewendet werden, um sie zu entmischen; d.h. Steigerung der Entropie entzieht dem System (arbeitsfähige) Energie Freie Energie ist die Energie, die in Arbeit (Knüpfung/Spaltung chem. Bindungen) umgesetzt werden kann Produkte werden häufig durch Folgereaktionen weiter umgesetzt, sodass in biosynthetischen Pathways immer eine „Richtung“ der Reaktion bevorzugt ist (i. d. R. die Hinreaktion) v.a. Pflanzen, dienen der Ernährung (Energieversorgung) tier. Organismen 28 In biologischen Systemen übernehmen Enzyme die Rolle von Biokatalysatoren 1850 Louis Pasteur, Hefe-Fermentation von Zucker in Alkohol durch Fermente 1897 Eduard Buchner, Hefeextrakte können Zucker zu Alkohol umsetzen, d.h. es bedarf keiner lebenden Zellen dazu 1926 James Sumner, Reinigung von Urease als erstem Enzym Proteasen sind Enzyme, die Peptidbindungen spalten Substratspezifität der Proteasen ist sehr unterschiedlich z.B. spaltet die Protease Trypsin PeptidBindungen nur C-terminal von Lys oder Arg während die Protease Thrombin nur die Peptidbindung zwischen Arg und Gly spaltet Trypsin Thrombin (Katalysator) k-1 Freie Energie, G E+S k+1 Fortschreitende Reaktion ES k+2 E+P E = Enzym S = Substrat ES = Enzym/Substratkomplex P = Produkt E+S k+1 k-1 ES k+2 E+P VMAX [S] V0 = k + [S] M Viele Enzyme benötigen für ihre Aktivität Cofaktoren Cofaktoren, die kleine organische Moleküle sind, werden als Coenzyme bezeichnet (viele Vitamine) Kovalent mit dem Apoenzym verbundene Coenzyme werden als Prosthetische Gruppen bezeichnet Die sechs Hauptenzymklassen The International Union of Biochemistry hat 1964 eine noch heute gültige Enzymnomenklatur erstellt, die jedem Enzym eine vierstellige Zahl (EC 1.1.1.1. oder EC 3.2.2.1) (EC steht für Enzyme Commission) zuweist ENZYME Enzyme nomenclature database http://us.expasy/org/enzyme ENZYME is a repository of information relative to the nomenclature of enzymes. It is primarily based on the recommendations of the Nomenclature Committee of the International Union of Biochemistry and Molecular Biology (IUBMB) and it describes each type of characterized enzyme for which an EC (Enzyme Commission) number has been provided [More details / References / Disclaimer]. Release 37, March 2005, and updates up to 26-Apr-2005 (4361 entries) Access to ENZYME •by EC number: ... •by enzyme class •by description (official name) or alternative name(s): •by chemical compound •by cofactor •by search in comments lines •SRS - Sequence Retrieval System ENZYME - The Enzyme Data Bank Search by enzyme class The following list contains the definitions of enzyme classes, subclasses and sub-subclasses. If you click on one of the following lines, you will get a list of all enzymes in the corresponding classes, with the possibility to obtain a list of all corresponding Swiss-Prot entries. View options: •display class only •display class and subclass •1. -. -.- Oxidoreductases. •1. 1. -.- Acting on the CH-OH group of donors. •1. 1. 1.- With NAD(+) or NADP(+) as acceptor. •1. 1. 2.- With a cytochrome as acceptor. •1. 1. 3.- With oxygen as acceptor. •1. 1. 4.- With a disulfide as acceptor. • 1. 1. 5.- With a quinone or similar compound as acceptor. •1. 1.99.- With other acceptors. •1. 2. -.- Acting on the aldehyde or oxo group of donors. •1. 2. 1.- With NAD(+) or NADP(+) as acceptor. •1. 2. 2.- With a cytochrome as acceptor. •1. 2. 3.- With oxygen as acceptor. •1. 2. 4.- With a disulfide as acceptor. ENZYME - The Enzyme Data Bank The following ENZYME entries belong to class 1.1.1.-: 1.1.1.1 Alcohol dehydrogenase. 1.1.1.2 Alcohol dehydrogenase (NADP+). 1.1.1.3 Homoserine dehydrogenase. 1.1.1.4 (R,R)-butanediol dehydrogenase. 1.1.1.5 Acetoin dehydrogenase. 1.1.1.6 Glycerol dehydrogenase. 1.1.1.7 Propanediol-phosphate dehydrogenase. … 1.1.1.280 (S)-3-hydroxyacid-ester dehydrogenase. 1.1.1.281 GDP-4-dehydro-6-deoxy-D-mannose reductase. 1.1.1.282 Quinate/shikimate dehydrogenase. ID 1.1.1.1 DE Alcohol dehydrogenase. AN Aldehyde reductase. CA An alcohol + NAD(+) = an aldehyde or ketone + NADH. CF Zinc or Iron. Acts on primary or secondary alcohols or hemiacetals. The animal, but not the yeast, enzyme acts also on cyclic secondary alcohols. Das aktive Zentrum von Enzymen ist die Region eines Enzyms, die das Substrat und ggf. den Cofaktor bindet und die Aminosäuren umfasst, die direkt am Trennen/Zusammenfügen chemischer Bindungen in Substrat/Produkt teilnehmen; diese nennt man auch katalytische Gruppen aktive Zentren können weit voneinander entfernte Aminosäurereste enthalten Aktive Zentren formen dreidimensionale Vertiefungen, in denen Substrate durch viele nichtkovalente Bindungen an das Enzym gebunden werden Die Bildung des Enzym-Substrat-Komplexes erfolgt nach dem Schlüssel-Schloss-Prinzip oder nach dem Prinzip des „induced fit“ Enzymatische Katalysemechanismen umfassen häufig zwei Substrate 1. Geordnete sequentielle Verdrängung (Lactat-Dehydrogenase) Geordnete, sequentielle Verdrängung heisst geordnete Substratbindung und danach Produktfreisetzung Enzymatische Katalysemechanismen umfassen häufig zwei Substrate 2. Ungeordnete sequentielle Verdrängung (Kreatin-Kinase) Substrate werden in zufälliger Sequenz gebunden und danach ungeordnet freigesetzt Enzymatische Katalysemechanismen umfassen häufig zwei Substrate 3. Doppelte Verdrängung (Pingpong-Reaktion) (Aspartat-Aminotransferase) Bindung des 1. Substrates und Freisetzung des 1. Produktes erfolgt vor Bindung des 2. Substrates Allosterische Enzyme und Kooperativität Allosterische Enzyme zeigen keine klassische Michaelis-Menten-Kinetik (hyperbole Abhängigkeit zwischen V und S) Enzyme, die aus mehreren Untereinheiten und damit aus mehreren aktiven Zentren aufgebaut sind, zeigen eine Sigmoidale V/S-Kinetik d.h. nach Bindung eines Substratmoleküls An eine Untereinheit wird die Bindung Eines 2. Substratmoleküls erleichtert (positive Kooperativität) Außerdem besitzen allosterische Enzyme häufig auch regulatorische Bindungsstellen, die nicht zum aktiven Zentrum gehören und die nach Bindung eines Regulators die Reaktionsgeschwindigkeit ebenfalls modulieren Können. Enzyme (E) können durch Inhibitoren (I) gehemmt werden Komp. Hemmg: I reagiert mit E Nichtkomp. Hemmung : I reagiert mit E und ES Unkomp. Hemmung : I reagiert mit ES Die verschiedenen Hemmtypen lassen sich kinetisch unterscheiden Lineweaver-Burk-Plots Komp. Hemmung Nichtkomp. Hemmung kM bei zunehmender Inhibitorkonz. veränderlich (größer) kM konstant Vmax wird bei steigender Inhibitorkonzentration veränderlich (kleiner) Vmax konstant Unkomp. Hemmung kM und Vmax mit steigender Inhibitorkonzentration verändert Irreversible Hemmung von Enzymen durch kovalente Modifikation des aktiven Zentrums durch gruppenspezifische Reagenzien (Cys/Ser-Reagenzien) Irreversible Hemmung von Enzymen durch kovalente Modifikation des aktiven Zentrums durch Substratanaloga