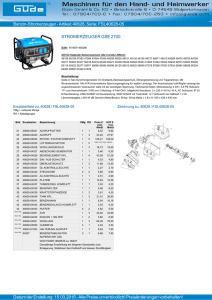
Frank Rutschmann
Werbung

Charakterisierung der
Ca2+-abhängigen Proteinkinase LeCPK1
aus Lycopersicon esculentum
Institut für Pflanzenwissenschaften der ETH Zürich
Biochemie und Physiologie der Pflanzen
Prof. Dr. N. Amrhein
Betreuer:
Dr. Andreas Schaller
Diplomarbeit
von Frank Rutschmann
Zürich,
im April 2001
ZUSAMMENFASSUNG
Die Calcium-abhängige Proteinkinase LeCPK1 aus Lycopersicon esculentum und zwei Cterminale Teilpeptide der Plasmamembran-H+-ATPase PMA2 von Nicotiana plumbaginifolia
wurden als GST-Fusionsproteine heterolog in E. coli exprimiert und anschliessend durch spezifische Bindung an eine Glutathion Sepharose-Matrix aus bakteriellen Extrakten gereinigt. Die
C-Termini der Plasmamembran-H+-ATPase wurden in vitro durch die LeCPK1 phosphoryliert.
Diese Phosphorylierungen waren Ca2+-abhängig und fanden an den C-Termini selbst statt und
nicht am GST-Anteil der Fusionsproteine. Sie wurden durch die allgemeinen ProteinkinaseInhibitoren Staurosporin und K-252a, nicht aber durch KN-62 und Bisindolmaleimid unterdrückt. Bei der Phosphorylierung von Plasmamembran-Vesikeln durch die LeCPK1 konnte
weder eine Aktivierung noch eine Inaktivierung der H+-ATPase nachgewiesen werden.
Ferner wurde die Bindung von Ca2+ an die LeCPK1 mittels Fluoreszenz-Spektrometrie untersucht, wobei sich hochaffine (Kd = 0.6 µM) und niedrigaffine (Kd = 55 µM) Bindestellen unterscheiden liessen. Durch Expression der Proteinkinase in einem in vitro Transkriptions/Translationssystem wurde gezeigt, dass die LeCPK1, nicht aber eine Gly2Ala-Mutante des
Enzyms N-terminal myristoyliert wird. Die Myristoylierung erwies sich als notwendig für eine
Lokalisation der LeCPK1 an der Plasmamembran. So liess sich die mit dem "Enhanced Green
Fluorescent Protein" fusionierte und in Allium cepa oder Lycopersicon peruvianum exprimierte
LeCPK1 im Bereich der Plasmamembran nachweisen, während die nicht-myristoylierte
Gly2Ala-Mutante im Cytosol und im Kern vorzufinden war.
II
INHALTSVERZEICHNIS
I. Einleitung
1.1 Die Plasmamembran-H+-ATPase
1
1.2 Regulation der Plasmamembran-H+-ATPase
4
1.2.1
1.2.2
1.2.3
1.2.4
+
Die H -ATPase wird durch die Bindung von 14-3-3-Proteinen aktiviert
Auch Lysophosphatidylcholin aktiviert die Plasmamembran-H+-ATPase
Die H+-ATPase wird durch Phosphorylierung auch deaktiviert
Hypothetisches Modell der Regulation der H+-ATPase
1.3 Die Rolle von Ca2+-abhängigen Proteinkinasen für die Phosphorylierung
der Plasmamembran-H+-ATPase
1.4 Vorausgehende Arbeiten und Zielsetzung
4
6
7
7
9
12
II. Materialien und Methoden
2.1 Pflanzen, Bakterienstämme und Vektoren
13
2.2 Medien
15
2.3 Chemikalien
2.3.1
2.3.2
2.3.3
2.3.4
2.3.5
2.3.6
PCR, Plasmid-DNA-Isolierung und Agarosegel-Elektrophorese
DNA-Sequenzierung
Glutathion Sepharose-Affinitätschromatographie
SDS-PAGE
TRICIN-SDS-PAGE
Verschiedenes
17
18
18
19
20
21
2.4 Methoden
2.4.1
2.4.2
2.4.3
2.4.4
2.4.5.
2.4.6
2.4.7
2.4.8
2.4.9
2.4.10
2.4.11
2.4.12
2.4.13
2.4.14
Expression und Isolierung der GST-Fusionsproteine in/aus E. coli
Reinigung der GST-Fusionsproteine
In vitro-Phosphorylierung der mit GST fusionierten C-Termini der H+-ATPase
In vitro-Phosphorylierung des C-Terminus der H+-ATPase (CT66)
Aktivitätsbestimmung der Plasmamembran-H+-ATPase
Amplifizierung der cDNAs CDPKwt und CDPKmut mittels PCR
Ligation der amplifizierten cDNAs in die Vektoren pBluescript SK(-) und pcl60
Transformation von kompetenten E. coli-Zellen
Isolierung von Plasmid-DNA (Mini Prep) aus E. coli
Analyse der Ligationsprodukte durch Restriktion der Plasmid-DNA
DNA-Sequenzanalyse
Amplifizierung und Isolierung der Konstrukte in/aus E. coli (Midi Prep)
In vitro-Transkription/Translation und Myristoylierung der LeCPK1
Transformation von Zwiebelepidermiszellen und transiente Expression
der Fusionsproteine CDPKwt-EGFP und CDPKmut-EGFP
2.4.15 Transformation von Lycopersicon peruvianum-Suspensionskulturzellen und
transiente Expression der Fusionsproteine CDPKwt-EGFP und CDPKmut-EGFP
2.4.16 Titration einer GST-CDPK-Lösung mit CaCl2 unter paralleler Aufnahme
des Fluoreszenz-Spektrums
III
22
22
23
24
25
26
27
28
28
29
29
29
30
31
32
33
III. Resultate
3.1 Expression und Aufreinigung der GST-Fusionsproteine GST-CT56 und GST-CT66
sowie des GST-Proteines selbst
34
3.2 In vitro-Phosphorylierung der Plasmamembran-H+-ATPase
37
3.3 Phosphorylierung des vom GST-Peptid abgetrennten C-Terminus der
Plasmamembran-H+-ATPase
39
3.4 Die Wirkung von Proteinkinase-Inhibitoren auf die Phosphorylierung
des C-Terminus der Plasmamembran-H+-ATPase
41
3.5 Der Einfluss einer Phosphorylierung der H+-ATPase auf die Aktivität der Protonenpumpe
44
3.6 In vitro-Transkription-/Translation und Myristoylierung der LeCPK1
48
3.7 Transiente Expression der Fusionsproteine CDPKwt-EGFP und CDPKmut-EGFP
in Zwiebelepidermiszellen
52
3.8 Transiente Expression der Fusionsproteine CDPKwt-EGFP und CDPKmut-EGFP
in Lycopersicon peruvianum-Zellen aus Suspensionskultur
55
3.9 Titration einer GST-CDPK-Lösung mit CaCl2 unter paralleler Aufnahme
des Fluoreszenzspektrums
57
IV. Diskussion
59
4.1 Die Bindung von Calcium an die LeCPK1
60
4.2 Subzelluläre Lokalisation der LeCPK1
64
+
4.3 Phosphorylierung der Plasmamembran-H -ATPase
68
4.4 Die Rolle der LeCPK1 in pflanzlichen Abwehrreaktionen
72
V. Literatur
74
VI. Anhang
6.1 Sequenz der LeCPK1-cDNA
81
+
6.2 Standardkurve für die Aktivitätsbestimmung der Plasmamembran-H -ATPase
IV
83
1. Einleitung
Seite 1
I. EINLEITUNG
1.1 Die Plasmamembran-H+-ATPase
Die Plasmamembran-H+-ATPase spielt in der Physiologie von Planzen und Pilzen eine Schlüsselrolle. Sie gehört zu der grossen, ubiquitären Familie von P-Typ-ATPasen, welche Kationen
wie K+ und Na+ (Tiere), Cd2+ und Cu2+ (Bakterien) und Ca2+ (Pilze, Pflanzen, Tiere) durch
Zellmembranen transportieren (Palmgren et al., 1998). Die Plasmamembran-H+-ATPase von
Pflanzen und Pilzen koppelt die Hydrolyse von ATP mit dem Protonentransport durch die
Plasmamembran. Ein solcher Transport verursacht sowohl eine pH-Differenz (? pH) als auch
eine Membranpotentialdifferenz (? E), welche beide Komponenten der protonenmotorischen
Kraft (proton motive force, pmf oder ? p) darstellen. Dieser elektrochemische Gradient treibt
dann sekundär aktivierte Transporter an, welche Ionen oder andere Verbindungen entgegen
ihres Konzentrationsgradienten durch die Membran transportieren.
Solche Transporter sind entweder Kanäle, welche mit grosser Geschwindigkeit Ionen befördern
und deren Öffnung häufig durch das Membranpotential reguliert wird. Oder es sind Carrier,
welche selektiv Makromoleküle und organische Verbindungen wie Zucker oder Aminosäuren
im Uniport, Symport oder Antiport mit Protonen durch die Membran schleusen (Ward et al.,
1998). Die beschriebenen Transportvorgänge bilden die Grundlage von vielen adaptiven Vorgängen in Pflanzen gegenüber sich verändernden Umweltbedingungen.
So transportieren zum Beispiel Pflanzen mit hoher Salztoleranz überschüssiges cytosolisches
Na+ durch einen Na+/H+-Antiport entweder in die Vakuole oder ganz aus der Zelle heraus (Niu
et al., 1995). Auch die Regulation des Turgordrucks (Osmoregulation) wird durch eine sekundär aktive Aufnahme von Ionen in die Zelle ermöglicht, angetrieben durch den von der Plasmamembran-H+-ATPase aufrecht erhaltenen Protonengradienten. Die dadurch erzielte höhere
Salzkonzentration im Zellinnern bewirkt einen Wassereinstrom in die Zelle und einen Anstieg
des Zellturgors. Auf diese Weise können beispielsweise Schliesszellen von Spaltöffnungen in
kurzer Zeit anschwellen und so eine Öffnung der Stomata bewirken (MacRobbie, 1998). Durch
Veränderung des Zellturgors werden auch Blattbewegungen (Ausrichtung der Blattflächen
nach der Sonne oder seismonastische Reaktionen, z.B. bei Mimosa pudica) möglich.
1. Einleitung
Seite 2
Eine weitere Rolle der Plasmamembran-H+-ATPase liegt in der Zellexpansion. Gemäss der
Säurewachstums-Theorie wird nach einem Auxin-Stimulus durch eine Ansäuerung des
Apoplasten die Zellwand plastisch verformbar und es kommt aufgrund des Turgordruckes zu
einer Zunahme des Zellvolumens. An diesen Vorgängen ist die Plasmamembran-H+-ATPase
mitbeteiligt (Cosgrove, 1997). In welcher Weise Auxin aber dieses Säurewachstum initiiert und
über welche Transduktionswege die "Wachstumssignale" vermittelt werden, ist noch unbekannt.
Die Plasmamembran-H+-ATPase ist ein integrales Membranprotein, dessen Monomer aus zehn
Transmembranhelices und vier cytoplasmatischen Bereichen besteht (Abb. 1). Sowohl der C-,
als auch der N-Terminus liegen auf der cytoplasmatischen Seite (Auer et al., 1998). Obwohl
die Quartärstruktur noch nicht aufgeklärt wurde, geht man davon aus, dass das Protein hauptsächlich als Dimer vorkommt (Bowman et al., 1985), wobei aber bereits das Monomer mit einer Masse von ca. 100 kDa katalytisch aktiv ist (Goormaghtigh et al., 1986). Der Mechanismus
des Protonentransportes ist bislang unbekannt. Durch Mutantenanalysen weiss man aber, dass
die kleine cytoplasmatische Schleife (Abb. 1) für die Kopplung der ATP-Hydrolyse mit dem
Protonentransport verantwortlich ist (Wach et al., 1996). Der grosse cytoplasmatische Loop
enthält einen für P-Typ-ATPasen typischen Aspartat-Rest (Asp536 in Abb. 1), welcher während
des katalytischen Zyklus phosphoryliert wird. Ausserdem befindet sich dort auch die ATPbindende Region (Pardo und Slayman, 1988). Während über die Funktion der N-terminalen
Region wenig bekannt ist, weiss man, dass die C-terminale Region als autoinhibitorische Domäne und dadurch als wichtiger Regulator der Plasmamembran-H+-ATPase wirkt (Palmgren et
al., 1990).
1. Einleitung
Seite 3
A
zielgerichtete Mutationen
bei der PMA2 von
Nicotiana plumbaginifolia
B
zielgerichtete Mutationen
bei der PMA1 von
Saccharomyces cerevisiae
Abb. 1: Struktur der Plasmamembran-H+-ATPasen PMA1 von Saccharomyces cerevisiae und PMA2 von
Nicotiana plumbaginifolia.
Die Funktion der durch Dreiecke und Kreise hervorgehobenen Aminosäuren wurde durch zielgerichtete Mutationen untersucht, die zum Austausch bzw. zur Deletion dieser Aminosäuren führten. Die in Quadern angegebenen
Aminosäuren sind konserviert und beiden Protonenpumpen gemeinsam (nach Portillo, 2000; Morsomme und
Boutry, 2000; Morsomme et al., 2000).
.
A: Kleine cytosolische Schleife; hier findet u.a. die Kopplung der ATP-Hydrolyse mit dem H+-Transport statt.
B: Grosse cytosolische Schleife; an dieser katalytische Domäne wird ATP gebunden und hydrolysiert. Dabei bildet Asp536 das für P-Typ-ATPasen typische intermediäre Aspartyl-Phosphat.
C: C-terminale Domäne; besitzt autoinhibitorische, regulatorische Funktionen und kann 14-3-3-Proteine binden.
N: N-terminale Domäne; besitzt regulatorische, noch weitgehend unverstandene Funktionen.
Das Enzym verwendet als Substrat MgATP, dessen Hydrolyse eng mit dem Protonentransport
verknüpft ist. Die meisten Isoformen des Proteins arbeiten optimal bei einem pH von 6.6 und
besitzen eine spezifische Aktivität in gereinigten Plasmamembranen von 1 bis 2 µmol Pi
/min/mg. Der Km-Wert für MgATP variiert zwischen 0.3 und 1.4 mM (Vara und Serrano,
1982).
Die Plasmamembran-H+-ATPase wird von einer Multigenfamilie codiert. So wurden u.a. in
Arabidopsis thaliana zwölf Gene identifiziert, in Nicotiana plumbaginifolia neun und in Lycopersicon esculentum sieben. Die codierenden Sequenzen können in zwei Subfamilien eingeteilt werden, deren Trennung schon vor der evolutiven Aufspaltung der Samenpflanzen in Monocotyledonen und Dicotyledonen erfolgte (Moriau et al., 1993).
1. Einleitung
Seite 4
Die einzelnen Isoenzyme der H+-ATPase werden in der Pflanze je nach Zelltyp, Gewebe, Entwicklungsstadium und Umweltbedingungen differenziell exprimiert, wobei verschiedene Isoformen in der gleichen Zelle koexistieren können. Northern Blots, in situ-Hybridisierungen
und Untersuchungen mit Antikörpern zeigten, dass Plasmamembran-H+-ATPasen u.a. in Wurzelhaaren, der Wurzelhaube, in der Blatt-Epidermis, in Schliesszellen, im Leitgewebe, in Pollenkörnern, im Tapetum der Antheren und in sich entwickelnden Samen vorkommen, wobei es
lokal zu starken Anhäufungen kommen kann (Morsomme und Boutry, 2000).
1.2 Regulation der Plasmamembran-H+-ATPase
Wie schon erwähnt, kann die Expression der Plasmamembran-H+-ATPase abhängig von Zelltyp, Gewebe, Entwicklungsstadium und Umweltbedingungen stark variieren, sowohl in der
Menge translatierten Proteins als auch in der Zusammensetzung der exprimierten Isoformen.
Zusätzlich zur transkriptionellen und posttranslationellen Regulation besteht eine weitere Möglichkeit der Regulation in der Steuerung der Aktivität bereits vorhandener Enzyme.
1.2.1 Die Plasmamembran-H+-ATPase wird durch die Bindung von 14-3-3-Proteinen
aktiviert
Die Plasmamembran-H+-ATPase besitzt eine C-terminale Region (Abb. 1), welche das Enzym
autoinhibieren kann. Entfernt man z.B. die letzten 51 Aminosäuren des C-Terminus der H+ATPase AHA2 von Arabidopsis thaliana durch Trypsinbehandlung oder durch genetische Deletion, so steigt die katalytische Effizienz, d.h. der Km-Wert für das Substrat MgATP sinkt und
vmax nimmt zu (Palmgren et al., 1990). Ferner wurde festgestellt, dass es zu einer Steigerung
der H+-ATPase-Aktivität nach Bindung von 14-3-3-Proteinen kommt (Oecking et al., 1997;
Jahn et al., 1997). Erst kürzlich wurde gezeigt, dass diese 14-3-3-Proteine direkt an die Cterminale Region binden, und zwar an die zweitletzte, in allen H+-ATPasen konservierte Aminosäure, das Threonin947 der H+-ATPase PMA2 von Nicotiana plumbaginifolia (Svennelid et
al., 1999; Maudoux et al., 2000).
1. Einleitung
Seite 5
14-3-3-Proteine sind hochkonservierte, ubiquitär in eukaryotischen Zellen vorhandene Proteine,
welche andere Enzyme und Transkriptionsfaktoren in ihrer Aktivität modulieren können (Finnie et al., 1999). Für die Interaktion mit 14-3-3-Proteinen haben sich wenige KonsensusMotive als wichtig erwiesen, in welchen sich oft phosphorylierte Aminosäuren befinden (Finnie et al., 1999; Moorhead et al., 1999). 14-3-3 Proteine treten meist als Dimere auf und können so zwei Zielmoleküle gleichzeitig binden und diese durch Assoziation regulieren.
Das Bindungsmotiv für 14-3-3-Proteine am C-Terminus der Plasmamembran-H+-ATPase
PMA2 von Nicotiana plumbaginifolia lautet ...QQxYTV (Abb. 27 auf Seite 69). Eine 14-3-3Bindung an diese Domäne ist nur dann möglich, wenn das hervorgehobene Threonin phosphoryliert vorliegt (Camoni et al., 1999; Svennelid et al., 1999; Fuglsang et al., 1999). Es zeigte
sich aber, dass in Anwesenheit von Fusicoccin (einem Toxin des Pilzes Fusarium amygdalii)
eine Phosphorylierung des Threonins für eine 14-3-3-Protein-Bindung an den C-Terminus nicht
notwendig ist, da Fusicoccin den 14-3-3-Protein-H+-ATPase-Komplex offenbar genügend stabilisiert. Allerdings kann eine solche phosphorylierungs-unabhängige 14-3-3-Bindung durch
ein kompetitierendes, ATPase-ähnliches Peptid viel leichter verhindert werden, als wenn das
Threonin phosphoryliert vorliegt (Svennelid et al., 1999). Nach gegenwärtiger Vorstellung
macht die Plasmamembran-H+-ATPase nach Bindung eines oder mehrerer 14-3-3-Proteine an
ihren C-Terminus eine Konformationsänderung durch, durch die es zur Aktivierung des Enzyms kommt (Abb. 2).
Kürzlich ist allerdings gezeigt worden, dass sich die beiden Subfamilien von pflanzlichen
Plasmamembran-H+-ATPasen hinsichtlich dieser C-terminalen Regulation unterscheiden
könnten. Während die zur Subfamilie I gehörende Isoform PMA2 aus Nicotiana plumbaginifolia dem obigen Regulationsmechanismus unterworfen ist, wird die PMA4 aus Nicotiana plumbaginifolia, welche der Subfamilie II angehört, am zweitletzen, C-terminalen Threonin nur
schwach phosphoryliert und in ihrer Aktiviät nur geringfügig moduliert. Ausschlaggebend für
diese differenzielle Regulation ist der viertletzte, konservierte Aminosäure-Rest am C-Terminus, der bei der H+-ATPasen der Subfamilie I ein Serin, bei jenen der Subfamilie II aber ein
Histidin darstellt (Damly und Boutry, 2001).
1. Einleitung
Seite 6
Abb. 2: Modell der Aktivierung von H+ATPasen durch Fusicoccin (Oecking et al.,
1997).
A: Zwei Plasmamembran-H+-ATPasen assoziieren und bilden ein aktives Dimer.
+
Die Aktivität der H -Pumpe wird durch den
autoinhibitorischen Effekt der C-Termini aber
limitiert.
B: 14-3-3-Protein-Dimere binden an die autoinhibitorischen C-Termini der H+-ATPasen
und bilden einen transienten Komplex, an
dem möglicherweise noch weitere Proteine
beteiligt sind. Dadurch wird die Aktivität des
Enzyms erhöht.
C: Fusicoccin-Bindung stabilisiert den Komplex und hält die H+-ATPase im aktiven Zustand.
(Taiz und Zeiger, 1998)
1.2.2 Auch Lysophosphatidylcholin aktiviert die Plasmamembran-H+-ATPase
Es wurde gezeigt, dass auch Lysophosphatidylcholin (LPC) die H+-ATPase aktivieren kann
(Pedchenko et al., 1990; Palmgren et al., 1991). Die Bindestelle der H+-ATPase für LPC
konnte aber bisher noch nicht ermittelt werden (Gomes et al., 1996; Morsomme et al., 1998).
Lysophosphatidylcholin (LPC) entsteht durch die Spaltung von Phosphatidylcholin in LPC und
freie Fettsäuren. Diese Reaktion wird durch das in Pflanzen vorhandene Enzym Phospholipase
A2 katalysiert. Die Phospholipase A2 (PLA2) ist bekannt als ein wichtiger Regulator in tierischen Systemen, der unter anderem den ersten Schritt der Eicosanoid-Biosynthese katalysiert.
In Pflanzen wird eine Beteiligung der PLA2 an Wundabwehr-Reaktionen postuliert (Narvaez-
1. Einleitung
Seite 7
Vasquez et al., 1999). Das Enzym könnte via LPC als second messenger auch an der Regulation der H+-ATPase beteiligt sein.
1.2.3 Die Plasmamembran-H+-ATPase wird durch Phosphorylierung auch deaktiviert
Im Gegensatz zu den bisher erwähnten Resultaten gibt es auch einige Experimente, welche
zeigen, dass eine Phosphorylierung der Plasmamembran-H+-ATPase nicht zu einer Aktivierung, sondern zu einer Inaktivierung der Protonenpumpe führen kann.
Schon 1988 wurde gezeigt, dass eine Plasmamembran-H+-ATPase aus Wurzelzellen von Avena
sativa an Serin- und Threonin-Resten calciumabhängig phosphoryliert wird (Schaller und
Sussman, 1988). Ausserdem wurde gezeigt, dass eine H+-ATPase von Lycopersicon esculentum von einer membrangebundenen Phosphatase dephosphoryliert und dadurch aktiviert werden kann. Diese Aktivierung erfolgte in Abhängigkeit eines Elicitors von Cladosporium fulvum. Nach Entfernen des pilzlichen Elicitors nahm die H+-ATPase-Aktivität wieder ab in Abhängigkeit einer Rephosphorylierung, welche durch verschiedene Proteinkinasen in zwei
Schritten durchgeführt wurde. Am ersten Phosphorylierungsschritt ist vermutlich eine Proteinkinase C-ähnliche Kinase, am zweiten eine Ca2+/Calmodulin-abhängige Proteinkinase (CaMKII oder CCaMK) beteiligt, wobei der zweite Schritt nicht ohne vorausgegangenen ersten
Schritt ablaufen kann (Xing et al., 1996). Auch in vitro-Experimente mit Membranfraktionen
aus Nicotiana plumbaginifolia (Desbrosses et al., 1998) und mit rekonstituierten Proteoliposomen aus Beta vulgaris (Lino et al., 1998) zeigten, dass eine Dephosphorylierung die Plasmamembran-H+-ATPase aktivieren kann, während eine Ca2+-abhängige Phosphorylierung das
Enzym deaktiviert.
1.2.4 Hypothetisches Modell der Regulation der H+-ATPase
Wie oben dargestellt wurde, kann eine Phosphorylierung der H+-ATPase sowohl zu einer Steigerung, als auch zu einer Verminderung der protonen-pumpenden Aktivität des Enzyms führen.
Nach Morsomme (2000) hat die H+-ATPase in nicht-phosphoryliertem Zustand eine geringe
Grundaktivität (Abb. 3a), die durch Phosphorylierung ausserhalb des C-Terminus weiter vermindert wird (Abb. 3b). C-terminale Phosphorylierung des Enyzms hingegen ermöglicht die
Bindung von 14-3-3-Proteinen sowie Dimerisierung und resultiert in einer Aktivierung der H+-
1. Einleitung
Seite 8
Pumpe (Abb. 3c). Weitere Phosphorylierung des C-Terminus hat möglicherweise eine Dissoziation der 14-3-3-Proteine zur Folge (C. Oecking, Bochum, pers. Mitteilung).
A
Abb. 3: Hypothetisches Modell der Regulation der Plasmamembran- H+-ATPase (Morsomme und Boutry, 2000).
A: Im nicht-phosphorylierten Zustand besitzt die Plasmamembran-H+-ATPase eine niedrige Grundaktivität.
B: Phosphorylierung der Plasmamembran-H+-ATPase an einer
bisher nicht ermittelten Stelle ausserhalb des C-Terminus (als
rotes Viereck dargestellt) führt zur Inaktivierung der Protonenpumpe.
B
C
C: Phosphorylierung an der zweitletzten Aminosäure des CTerminus ermöglicht die Bindung eines 14-3-3-ProteinDimers und führt zur Aktivierung des Enzyms. Eine vergleichbar starke Aktivierung wie durch 14-3-3-Proteine ist auch
durch Bindung von Lysophosphatidylcholin (LPC, als Dreieck
dargestellt) an einer unbekannten Stelle (evtl. ausserhalb des
C-Terminus) möglich.
Der hier orangefarben dargestellte Abschnitt des C-Terminus
ist für die Autoinhibierung der Protonenpumpe durch Bindung
an die katalytische Domäne verantwortlich, während der blau
markierte Bereich das 14-3-3-Dimer binden kann.
1. Einleitung
Seite 9
1.3 Die Rolle von Ca2+-abhängigen Proteinkinasen für die Phosphorylierung
der Plasmamembran-H+-ATPase
Viele der oben beschriebenen Phosphorylierungen der Plasmamembran-H+-ATPase sind Ca2+abhängig. Durch Einsatz von spezifischen Inhibitoren kann der Typ der beteiligten Kinase bestimmt werden. So wurde kürzlich eine Plasmamembran-assoziierte Proteinkinase aus Wurzelzellen von Zea mays gereinigt und festgestellt, dass sie eine Ca2+-abhängige Aktivität aufwies.
Das Enzym war in der Lage, die Plasmamembran-H+-ATPase in vitro am C-Terminus zu phosphorylieren (Camoni et al., 1998). Die Kinase konnte durch Calmodulin nicht aktiviert, aber
durch Calmodulin-Antagonisten inhibiert werden. Diese Eigenschaften sind typisch für eine
Ca2+-abhängige Proteinkinase (Ca2+-dependent protein kinase, auch calmodulin-like domain
protein kinase genannt).
Ca2+-abhängige Proteinkinasen (CDPKs) sind Enzyme, die bisher nur in Pflanzen und Protozoen, nicht aber in Hefen oder im Tierreich gefunden wurden (Hunter und Plowman, 1997). Sie
sind die einzigen pflanzlichen Proteinkinasen, die durch Ca2+ direkt aktiviert werden. Es existieren zahlreiche Isoformen des Enzyms (alleine in Arabidopsis thaliana sind es 39), welche in
bisher sieben Subfamilien eingeteilt werden (Satterlee und Sussman, 1998; Harmon et al.,
2000). Die CDPKs besitzen eine katalytische Domäne mit Serin/Threonin-ProteinkinaseAktivität (Stone und Walker, 1995). Diese katalytische Domäne wird in Abwesenheit von Ca2+
durch eine autoinhibitorische Domäne inaktiviert. Eine benachbarte Calmodulin-ähnliche Domäne enthält bis zu vier EF-Hand-Motive und ist damit fähig, freie Ca2+-Ionen zu binden (Abb.
4). Es wird postuliert, dass durch diese Ca2+-Bindung die Calmodulin-ähnliche Domäne eine
unmittelbar benachbarte Region der autoinhibitorischen Domäne binden kann, wodurch das
Enzym aktiviert wird (Binder et al., 1994; Harmon et al., 1994; Yoo und Harmon, 1996).
Eine weitere, variable Domäne unbekannter Funktion am N-Terminus enthält bei den meisten
CDPK-Isoformen ein N-Myristoylierungs-Motiv. An ein Glycin, das Teil dieses Motives ist,
wird während der Translation Myristinsäure (eine gesättigte C14-Fettsäure) kovalent über eine
Peptidbindung gebunden (Russell et al., 1994). Diese Modifizierung vergrössert die Hydrophobizität des N-Terminus und könnte zusammen mit weiteren posttranslationellen Änderungen
(siehe Abschnitt 4.2) zur Verankerung der CDPK in Zellmembranen führen (Yalovsky et al.,
1999). Tatsächlich wurden schon CDPKs von Hordeum vulgare (Klimczak und Hind, 1990),
Avena sativa (Schaller et al., 1992), Nicotiana plumbaginifolia (Iwata et al., 1998) und Oryza
sativa (Martin und Busconi, 2000) aus Plasmamembran-Fraktionen gereinigt.
1. Einleitung
Seite 10
Zu den bisher identifizierten membranständigen Substraten der CDPKs gehören u.a. die schon
erwähnte Plasmamembran-H+-ATPase von Avena sativa (Schaller und Sussman, 1988) und
Zea mays (Camoni et al., 1998), ein Tonoplasten-Wasserkanal (a-TIP) von Arabidopsis thaliana (Johnson und Chrispeels, 1992), ein Vakuolen-Chlorid-Kanal in Schliesszellen von Vicia
faba (Pei et al., 1996), eine Ca2+-Pumpe (ACA2) in der ER-Membran von Arabidopsis thaliana
(Hwang et al., 2000) und Nodulin-26, ein integraler Membrantransporter in der PeribakteroidMembran von N-fixierenden Bakterien in Wurzelknöllchen von Glycine maximus (Weaver et
al., 1991). Zwei gut charakterisierte cytosolische Substrate sind die Nitrat-Reduktase (Douglas
et al., 1998) und die Sucrosephosphat-Synthase (McMichael, 1995) aus Blättern von Spinacea
oleracea. Beide Substrate können durch dieselbe CDPK (AtCPK3 aus Arabidopsis thaliana)
phosphoryliert und damit inaktiviert werden (McMichael, 1995). Es ist also denkbar, dass eine
einzige CDPK diese zwei wichtigen Schlüsselenzyme reguliert. Allerdings lassen die vielen
existierenden Isoformen in ein und derselben Pflanze auf indivuelle Rollen der einzelnen
CDPKs in verschiedenen Signaltransduktions-Kaskaden schliessen (Harmon et al., 2000).
1. Einleitung
Seite 11
1
Variable Domäne
MGGCFSKKYT QQDANGHRAG RRVNQAYQKP PQPQPERPYQ PQPQQERPYQ
51
PPPQPAYQPP PQPKPQPQPH PVPVTVQSGQ PQDQMQGPHM NNILGKPFEE
101
Katalytische Domäne
IRKLYTLGKE LGRGQFGVTY YCTENSTGNP YACKSILKRK LVSKNDREDM
151
KREIQIMQHL SGQPNIVEFK GAYEDRQSVH LVMELCAGGE LFDRIIARGY
201
YSEKDAAEII RQIVNVVNIC HFMGVMHRDL KPENFLLTSK DENAMLKATD
251
FGLSVFIEEG KVYRDIVGSA YYVAPEVLRR SYGKEADVWS AGVILYILLS
301
GVPPFWAETE KGIFNTILKG EIDFQSDPWP SISNSAKDLI RKMLTQEPRK
351
Autoinhibitorische Domäne
RITSAQVLEH PWLRLGEASD KPIDSAVLSR MKQFRAMNKL KKLALKVIAE
401
EF-Hand
NLSEEEIKGL KAMFHNIDTD NSGTITYEEL KSGLARLGSK LTETEVKQLM
451
EF-Hand
EF-Hand
EAADVDGNGS IDYIEFITAT MHRHRLERDE HLFKAFQHFD KDHSGFITRD
501
EF-Hand
ELENAMKEYG MGDEATIKEI IAEVDTDNDG RINYEEFCAM MRSGTTQPQQ
551
KLF
Abb. 4: Die Aminosäuresequenz der LeCPK1 aus Lycopersicon esculentum. Die verschiedenen Funktionen der
markierten Domänen werden im Text näher erläutert. Die Position der durch Fettdruck hervorgehobenen Tryptophan-Reste innerhalb der dreidimensionalen Struktur der LeCPK1 wirkt sich auf die im Abschnitt 3.9 gemessene
Fluoreszenz der Proteinlösung aus.
1. Einleitung
Seite 12
1.4 Vorausgehende Arbeiten und Zielsetzung
Im Rahmen der dieser Arbeit vorausgehenden Diplomarbeit (Stalder, 2000) wurde eine CDPK
aus einer cDNA-Bibliothek von Lycopersicon esculentum kloniert und sequenziert. Die
LeCPK1 benannte Kinase weist eine hohe Aminosäuresequenz-Ähnlichkeit (94 %) mit der
NtCPK1 aus Nicotiana tabacum (Yoon et al., 1999) auf. Sie besteht aus 553 Aminosäuren und
besitzt die klassischen Domänen einer CDPK, u.a. eine Ca2+-bindende Domäne mit vier Ca2+Bindestellen (Abb. 4). Eine Northern Blot-Analyse zeigte, dass das Protein vor allem in Wurzeln, Blüten und noch undifferenzierten Zellen exprimiert ist, aber auch in den Kotyledonen
und Blättern. Während eine Verwundung der Tomatenblätter zu keinem höheren LeCPK1Transkriptspiegel führte, induzierte eine Fusicoccin-Behandlung der Pflanzen nach vier Stunden eine maximale Akkumulation der Transkripte. Die LeCPK1-cDNA wurde als GSTFusionsprotein (GST-CDPK) in E. coli exprimiert und aus bakteriellen Extrakten gereinigt. Für
die GST-CDPK wurde Ca2+-Bindung an die C-terminale Domäne nachgewiesen. Die Proteinkinase zeigte Ca2+-abhängige Autophosphorylierung an Serin- und Threonin-Resten und für die
Phosphorylierung des synthetischen Peptids Syntide-2 wurde ein Km-Wert zwischen 82 und 89
µM ermittelt.
Im Rahmen der vorliegenden Diplomarbeit sollte die Bindung von Ca2+ an die LeCPK1 charakterisiert werden. Ferner sollte geprüft werden, ob die Proteinkinase myristoyliert wird und
inwiefern sich dies auf die intrazelluläre Lokalisation des Proteins auswirkt. Ausserdem sollte
untersucht werden, ob die Plasmamembran-H+-ATPase ein Substrat der LeCPK1 ist und ob
eine mögliche Phosphorylierung sich auf die Aktivität der Protonenpumpe auswirkt.
2. Material und Methoden
Seite 13
II. MATERIALIEN UND METHODEN
2.1 Pflanzen, Bakterienstämme und Vektoren
Lycopersicon peruvianum
Suspensionskultur in Nover-Medium (zur Verfügung gestellt von D. Frasson, ETH Zürich).
Die Kulturen wurden wöchentlich passagiert und am Tag
der Passage aufgearbeitet.
Allium cepa
Küchenzwiebel (COOP, Zürich)
E. coli K12 PR745
Expressions-Stamm für die GST-CT56 und GST-CT66Fusionsproteine (zur Verfügung gestellt von C. Oecking,
Ruhr-Universität, Bochum).
E. coli TOP10'
F' {lacIq Tn10 (TetR)} mcrA ? (mrr-hsdRMSmcrBC) F 80lacZ? M15 ? lacX74 recA1 deoR
araD139 ? (ara-leu) 7697 galU galK rpsL (StrR) endA1
nupG
(Invitrogen One Shot®)
pGEX-4T-1
Ermöglicht die Expression eines GST-Fusionsproteins unter
Kontrolle des mit IPTG induzierbaren tac-Promoters. Die
proteolytische Spaltung des zu exprimierenden Proteins von
der GST-Domäne ist mit Thrombin möglich.
(Amersham Pharmacia Biotech)
pGEX-G
Derivat des pGEX-3X-Vektors
(Amersham Pharmacia Biotech)
Erlaubt die Expression eines GST-Fusionsproteins unter
Kontrolle des mit IPTG induzierbaren tac-Promoters. Die
proteolytische Spaltung des zu exprimierenden Proteins von
der GST-Domäne ist mit dem Faktor Xa möglich.
(Görlach und Schmid, 1996)
pSK
pBluescript SK(-) (Stratagene)
Ermöglicht die in vitro-Transkription einer cDNA unter der
Kontrolle des T7-Promotors durch die T7 RNAPolymerase.
2. Material und Methoden
pcl60
Seite 14
Derivat des pBluescript SK-Vektors (Stratagene)
Ermöglicht die transiente Expression eines fluoreszierenden
EGFP-Fusionsproteines (Enhanced Green Fluorescent Protein, Clontech) unter der Kontrolle des 35S-Promotors (aus
dem Cauliflower Mosaic Virus) in pflanzlichen Zellen (zur
Verfügung gestellt von Claudio Lupi, Biotechnologie der
Pflanzen, ETH Zürich).
2. Material und Methoden
Seite 15
2.2 Medien
Die Chemikalien stammen, sofern ihre Herkunft im Text nicht speziell erwähnt wird,
von Fluka, Buchs SG.
LB-Medium
25 g LB Broth, Miller
(DIFCO Laboratories, Detroit, MI, USA)
ddH2O ad 1 Liter
autoklaviert (20 min)
LBAmp Medium
(für Flüssigkulturen)
25 g LB Broth, Miller (DIFCO)
ddH2O ad 1 Liter
autoklaviert (20 min)
Nach Abkühlung (ca. 60 C°) Zugabe von
1 ml Ampicillin- Stocklösung (100 mg/ml, sterilfiltriert)
LBAmp Agar
(für Petrischalen)
25 g LB Broth, Miller (DIFCO)
20 g Agar (DIFCO)
ddH2O ad 1 Liter
autoklaviert (20 min)
Nach Abkühlung (ca. 60 C°) Zugabe von
1 ml Ampicillin Stocklösung (100 mg/ml, sterilfiltriert)
steril in Petrischalen abgefüllt
MS-Agar
(für Petrischalen)
4.43 g Murashige and Skoog-Medium (MS, Duchefa)
20 g Agar (DIFCO)
ddH2O ad 1 Liter
autoklaviert (20 min)
steril in Petrischalen abgefüllt
Nover-Medium
(für Flüssigkulturen)
44.3 g Murashige and Skoog-Medium,
Basal Salt with Minimal Organics (MSMO, Sigma)
30 g Sucrose
170 mg KH2PO4
5 mg a-Naphtylessigsäure (NAA)
2 mg N-Benzyladenin (BA)
1 ml Vitamine AT 1000x
ddH2O ad 10 Liter
autoklaviert (20 min)
2. Material und Methoden
Seite 16
Plasmolyse-Agar
(für Petrischalen)
44.3 g Murashige and Skoog-Medium,
Basal Salt with Minimal Organics (MSMO, Sigma)
100 g Sucrose
170 mg KH2PO4
5 mg a-Naphtylessigsäure (NAA)
2 mg N-Benzyladenin (BA)
1 ml Vitamine AT 1000x
20 g Agar (DIFCO)
ddH2O ad 1 Liter
autoklaviert (20 min)
steril in Petrischalen abgefüllt
Vitamine AT 1000x
(250 ml)
500 mg Vitamin B1-HCl
250 mg Nicotinsäure
25 mg p-Aminobenzoesäure
125 mg Pyridoxin-HCl
1250 mg Cholinchlorid
250 mg Calcium D(+)-Panthothenate
2.5 mg Folsäure (0.1 mg/ml in 0.1 N NaOH)
2.5 ml Biotin (0.1 mg/ml in 0.1 N NaOH)
2.5 ml Cyanocobalamin (0.1 mg/ml)
pH 6.2 mit KOH
ddH2O ad 250 ml
sterilfiltrieren
2. Material und Methoden
Seite 17
2.3 Chemikalien
Alle Lösungen wurden nach Sambrook et al. (1989) angesetzt.
2.3.1 PCR, Plasmid-DNA-Isolierung und Agarosegel-Elektrophorese
Polymerasen
Pwo DNA-Polymerase (Roche Diagnostics)
Taq DNA-Polymerase (Roche Diagnostics)
T7 RNA-Polymerase (Promega)
PCR-Puffer
2 mM MgSO4 (Roche Diagnostics)
1x Reaktionspuffer (Roche Diagnostics)
200 µM dNTP-Mix (MBI Fermentas)
Enzyme
EcoRI und EcoRI-Puffer (MBI Fermentas)
NotI und NotI-Puffer (MBI-Fermentas)
XbaI und Puffer Y (MBI-Fermentas)
T4 DNA-Ligase und 10x Ligationspuffer (MBI Fermentas)
Thrombin (Amersham Pharmacia Biotech)
Mini Prep-Puffer
25 mM Tris / HCl, pH 7.5
50 mM Glucose
10 mM EDTA
autoklaviert (20 min)
TE-Puffer
10 mM Tris / HCl, pH 8.0
1 mM EDTA
autoklaviert (30 min)
1x TAE
40 mM Tris / AcOH, pH 8.0
1 mM EDTA
autoklaviert (30 min)
50x TAE
242 g Tris
57.1 ml Essigsäure
100 ml 0.5 M EDTA, pH 8.0
ddH2O ad 1 Liter
autoklaviert (30 min)
0.8 % (w/v) Agarosegel
0.8 g Agarose (Eurobio)
100 ml ddH2O
2 ml 50x TAE
lösen unter erhitzen
10 µl EtBr (5 mg/ml)
2. Material und Methoden
Seite 18
6x DNA-Probenpuffer
0.25 % w/v Bromphenolblau
0.25 % w/v Xylencyanol FF
30 % Glycerin in Wasser
DNA-Marker
(200 µl)
140 µl TE-Puffer
20 µl 1 kb DNA Ladder (1 µg/µl, GIBCO BRL)
40 µl 6x DNA-Probenpuffer
1x Laufpuffer
(4 Liter)
80 ml 50x TAE
200 µl EtBr
ddH2O ad 4 Liter
2.3.2 DNA-Sequenzierung
Sequenziergelmix
SequaGel XR (National Diagnostics)
Ladepuffer
80 % Formamid
20 % 25 mM EDTA, pH 8.0
50 mg/ml Blue Dextran
10x TBE (Laufpuffer)
108 g Tris
55 g Borsäure
8.3 g EDTA, pH 8.0
ddH2O ad 1 Liter
autoklaviert (30 min)
2.3.3 Glutathion Sepharose-Affinitätschromatographie
Glutathion Sepharose 4B
10 ml geliefert in 20% (v/v) EtOH
(Amersham Pharmacia Biotech)
Puffer A
(30 ml)
10 mM NaCl
1 mM EDTA
50 mM Tris/HCl, pH 8.0
autoklaviert (30 min)
frisch dazugegeben:
– 1 mM PMSF
– 1 Spatelspitze DNAse (Promega)
Waschpuffer
50 mM Tris/HCl, pH 8.0
Elutionspuffer
10 mM reduziertes Glutathion (Roche Diagnostics)
50 mM Tris/HCl, pH 8.0
2. Material und Methoden
Seite 19
2.3.4 SDS-PAGE
30 % (w/v) Monomerengemisch
29.2 % (w/v) Acrylamid (Bio-Rad)
0.8 % (w/v) Bisacrylamid (Bio-Rad)
Trenngelpuffer
1.5 M Tris/HCl, pH 8.8
0.4 % (w/v) SDS
Sammelgelpuffer
0.5 M Tris/HCl, pH 6.8
0.4 % (w/v) SDS
SDS-Polyacrylamidgel
(10% w/v, zwei 1.5 mm Gele)
Trenngel:
6 ml 30% (w/v) Monomerengemisch (Bio-Rad)
7.5 ml ddH2O
4.5 ml Trenngelpuffer
60 µl Ammoniumpersulfat 10% (w/v, Amreco)
13.5 µl TEMED (Bio-Rad)
Sammelgel:
1.25 ml 30% (w/v) Monomerengemisch
5 ml ddH2O
2.1 ml Trenngelpuffer
25 µl Ammoniumpersulfat 10%
15 µl TEMED
2x SDS-Probenpuffer
(5 ml)
1.5 ml Sammelgelpuffer
1 ml 20 % (w/v) SDS
0.5 ml 87 % (v/v) Glycerin
0.5 ml ß-Mercaptoethanol
1 Spatelspitze Bromphenolblau
1.5 ml ddH2O
Protein-Marker
5 % (w/v) SDS-PAGE Standards, low range (Bio-Rad)
in SDS-Probenpuffer
10x SDS-Laufpuffer
(5 Liter)
150 g Tris/HCl, pH 8.3
720 g Glycin
50 g SDS
ddH2O ad 5 Liter
Gelfärbelösung
(1 Liter)
2.5 g Coomassie Brilliant Blue R 250
900 ml Methanol techn.
100 ml Essigsäure
Gelfixierlösung
(1 Liter)
600 ml ddH2O
300 ml MeOH techn.
100 ml Essigsäure
2. Material und Methoden
Seite 20
2.3.5 TRICIN-SDS-PAGE
49.5% (w/v) Monomerengemisch 240 g Acrylamid (Bio-Rad)
(500 ml)
7.5 g Bisacrylamid (Bio-Rad)
ddH2O ad 500 ml
Tris-HCl/SDS-Gelpuffer
(500 ml)
182 g Tris, pH 8.5
1.5 g SDS
ddH2O ad 500 ml
SDS-Polyacrylamidgel
(16.5% w/v, zwei 1.5 mm Gele)
Trenngel:
6.6 ml 49.5% (w/v) Monomerengemisch
4.4 ml ddH2O
6.6 ml Tris-HCl/SDS-Gelpuffer
2.4 ml 87% (v/v) Glycerol
100 µl Ammoniumpersulfat 10% (w/v)
10 µl TEMED (Bio-Rad)
Sammelgel:
1.0 ml 49.5% (w/v) Monomerengemisch
8.4 ml ddH2O
3.1 ml Tris-HCl/SDS-Gelpuffer
65 µl Ammoniumpersulfat 10% (w/v)
6.5 µl TEMED (Bio-Rad)
2x SDS-Probenpuffer
(10 ml)
1.0 ml 1M Tris, pH 6.8
4 ml 20 % (w/v) SDS
2.75 ml 87 % (v/v) Glycerin
0.4 ml ß-Mercaptoethanol
1 Spatelspitze Coomassie Brilliant Blue G 250
ddH2O ad 10 ml
1x Kathoden-Puffer
(1 Liter)
12.11 g Tris
17.92 g TRICIN
1 g SDS
ddH2O ad 1 Liter
5x Anoden-Puffer
(1 Liter)
121.1 g Tris, pH 8.9
ddH2O ad 1 Liter
2. Material und Methoden
Seite 21
2.3.6 Verschiedenes
Radioaktive Substanzen
[?-32P]-ATP (ICN), 4500 Ci/mmol
[35S]-Methionin (Hartmann Analytic), 1000 Ci/mmol
[9,10-3H]-Myristinsäure (Moravek Biochemicals),
50 Ci/mmol
Phosphatreagenz
Lösung 1:
337.5 mg Malachitgrün
ddH2O (ultrarein) ad 745 ml
Lösung 2:
10.5 g Ammoniumheptamolybdat [(NH4)6Mo7O24 · 4H2O]
4 M HCl ad 245 ml
Lösungen 1 und 2 mischen und während 24 h bei 4 °C
inkubieren
in Polyethylenflasche filtrieren
0.04 % (v/v) Tergitol NP-10 dazufügen
10x PBS
80 g NaCl
2 g KCl
14.4 g Na2HPO4
2.4 g KH2PO4
pH 7.4 mit HCl
ddH2O ad 1 Liter
autoklaviert (30 min)
2. Material und Methoden
Seite 22
2.4 Methoden
2.4.1 Expression und Isolierung der GST-Fusionsproteine in/aus E. coli
Zur Expression der Fusionsproteine GST-CT56 und GST-CT66 und des GST-Proteins selbst
(Glutathion S-Transferase) lagen pGEX-4T-1-Expressionsvektoren in Bakterienkolonien (E.
coli K12 PR745) auf LBAmp Agar-Petrischalen vor.
Mit einzelnen Kolonien wurden 2 ml LBAmp-Flüssigkulturen inokuliert und über Nacht bei 37
°C und 220 rpm geschüttelt. Anschliessend überführte man die Zellen in grössere 200 ml
LBAmp-Flüssigkulturen und zog sie wie zuvor bei 37 °C und 220 rpm bis zu einer optischen
Dichte (600 nm) von 0.8 an. Durch Zugabe von sterilem IPTG zu 1 mM wurde die Expression
der Fusionsproteine induziert. Nach 120 min bei 37 °C und 220 rpm wurden die Zellen abzentrifugiert (10 min, 7'700 x g, 4 °C) und der Überstand verworfen.
Das Zellsediment wurde dann jeweils mit Hilfe einer 10 ml Stabpipette in 10 ml Puffer A mit
zusätzlich 1 mg/ml Lysozym resuspendiert. Die Lyse erfolgte während 20 min auf Eis, gefolgt
vom mechanischen Zellaufschluss am Sonicator (W-380, Heat Systems, Ultrasonics). Dazu
wurde die Zellsuspension 5 x 30 s mit Ultraschall behandelt. Zelltrümmer sowie unlösliche
Proteine (u.a. in „Inclusion Bodies“) wurden durch Zentrifugation (10 min, 10'000 x g, 4 °C)
entfernt. Der Überstand wurde bis zu seiner Verwendung bei 4 °C gelagert. Aliquote davon
wurden mittels SDS-PAGE analysiert.
2.4.2 Reinigung der GST-Fusionsproteine
Das Reinigungsprinzip der Glutathion Sepharose-Affinitätschromatographie beruht auf der
Fähigkeit des GST-Anteils des Fusionsproteins, an die Glutathion Sepharose-Matrix zu binden.
Es wurden 300 µl Glutathion Sepharose 4B verwendet, was einem Bettvolumen von 200 µl
entspricht. Die Kapazität der Matrix beträgt 5 mg Fusionsprotein pro ml Bettvolumen (Angaben des Herstellers). In einem 15 ml Zentrifugenröhrchen wurden 9.7 ml Puffer A vorgelegt,
300 µl Glutathion Sepharose 4B dazugegeben und geschüttelt. Nach diesem Waschvorgang
wurde die Matrix abzentrifugiert (5 min, 500 x g, 4 °C), der Überstand verworfen und der zu
reinigende Proteinextrakt zugesetzt. Der Ansatz wurde dann im Überkopfschüttler während 30
min gemischt, die Matrix erneut abzentifugiert (5 min, 500 x g, 4 °C) und der Überstand verworfen. Anschliessend wurde dreimal mit je 15 ml Puffer A gewaschen, wieder zentrifugiert (5
2. Material und Methoden
Seite 23
min, 500 x g, 4 °C) und die Überstände jeweils verworfen. Dann wurden die Fusionsproteine
von der Matrix eluiert durch Zugabe von 500 µl Elutionspuffer, gefolgt von gründlichem Mischen während 1 min, Abzentrifugieren der Matrix (5 min, 500 x g, 4 °C) und Transferieren des
Überstands in ein 1.5 ml-Reaktionsgefäss. Diese Elution wurde fünfmal wiederholt. Nach der
Analyse der gereinigten Proteine mittels SDS-PAGE wurden Eluatfraktionen, die das Fusionsprotein enthielten, vereinigt, neu aliquotiert und bei –20 °C gelagert.
Die Bestimmung der Proteinkonzentration der gesammelten Elutatfraktionen erfolgte nach
Bradford (1976). Ein Farbreagenz (Coomassie Protein Assay Reagent, Pierce Chem. Co.), basierend auf Coomassie Brilliant Blue G 250, wurde 1:10 (v/v) mit der zu analysierenden Proteinlösung gemischt und anschliessend im Spektrophotometer bei einer Wellenlänge von 595
nm gemessen. Die Proteinkonzentrationen wurden anhand einer BSA-Eichgerade errechnet.
2.4.3 In vitro-Phosphorylierung der mit GST fusionierten C-Termini
der H+-ATPase (GST-CT56 und GST-CT66)
Jeder Teilversuch wurde in einem Totalvolumen von 15 µl durchgeführt, wovon 10 µl auf den
Reaktionspuffer entfielen: 50 mM HEPES pH 7.5, 10 mM MgCl2, 2 mM DTT, 5 µM ATP, 1
mM EGTA, 1.1 mM CaCl2 und ddH2O (alle angegebenen Konzentration beziehen sich auf das
Totalvolumen des Ansatzes von 15 µl). Um die Ca2+-Abhängigkeit der Reaktion zu testen,
wurde ein zweiter Reaktionspuffer vorbereitet, der kein CaCl2, dafür EGTA in einer Konzentration von 5 mM enthielt.
Nach der Zubereitung der Puffer wurde radioaktiv markiertes [?-32P]-ATP in einer Endkonzentration von 0.03 µM (4500 Ci/mmol) dazugegeben. Daraus resultierte eine spezifische Aktivität
im Ansatz von 5.8 * 105 dpm/pmol ATP. Anschliessend wurden die jeweis eingesetzten Proteine (GST-CDPK: je 0.4 µg, GST-CT56: je 2.7 µg, GST-CT66: je 1.9 µg, GST: je 0.9 µg) in 1.5
ml Reaktionsgefässen vorgelegt und die Reaktionen durch Zugabe des jeweiligen Puffers gestartet.
Nach der vorgesehenen Inkubationszeit von 1, 5 oder 25 min bei 25 °C wurden die Reaktionen
durch Zugabe von je 15 µl 2x SDS-Probenpuffer abgestoppt und die Proteine während 5 min
bei 95 °C denaturiert. Anschliessend wurden je 20 µl der Proben auf ein SDS-Polyacrylamidgel
(10 % w/v, Dicke 1.5 mm) geladen und bei 125 V aufgetrennt. Danach wurden die Proteinbanden während 30 min in Gelfärbelösung (basierend auf Coomassie Brilliant Blue R 250) gefärbt
und das Gel über Nacht in Gelfixierlösung schüttelnd entfärbt. Nach einer zweistündigen Inku-
2. Material und Methoden
Seite 24
bation in ddH2O wurde das Gel während 2 h bei 80 °C im Geltrockner getrocknet, ein Röntgenfilm aufgelegt und dieser nach einer Belichtungszeit von 3.5 h maschinell entwickelt.
Die Wirkung von Proteinkinase-Inhibitoren auf die Aktivität der GST-CDPK wurde mit wenigen Abweichungen auf gleiche Weise getestet. Den Teilversuchen wurden vor Reaktionsbeginn
zusätzlich 3 µM Fusicoccin (Sigma), 4 µM Staurosporin (Alexis), 2 µM K-252a (Alexis), 5 µM
KN-62 (Alexis) oder 0.2 µM Bisindolmaleimid (Alexis) zugegeben. Ausserdem wurden je 0.2
µg GST-CDPK und 2.8 µg GST-CT66 verwendet. Die Inkubationszeit betrug bei allen Teilversuchen 60 min bei 25 °C und die Proteine wurden auf einem SDS-Polyacrylamidgel (8 % w/v,
Dicke 1.5 mm) bei 125 V aufgetrennt.
2.4.4 In vitro-Phosphorylierung des C-Terminus der H+-ATPase (CT66)
Zunächst wurde der GST-Anteil vom Fusionsprotein GST-CT66 proteolytisch abgespalten.
Dazu wurden 35 µg Fusionsprotein mit 14 U Thrombin (1 µg/µl, Amersham Pharmacia Biotech) in 100 µl PBS während 3 h bei 25 °C inkubiert. Danach erfolgte die Phosphorylierung des
CT66-Peptides in einem Totalvolumen von je 20 µl. Davon entfielen je 2.5 µl auf den Reaktionspuffer: 50 mM HEPES pH 7.5, 10 mM MgCl2, 2 mM DTT, 5 µM ATP, 1 mM EGTA, 1.1
mM CaCl2 (alle angegebenen Konzentrationen beziehen sich auf das Endvolumen der Ansätze
von 20 µl). Um die Ca2+-Abhängigkeit der Reaktion zu testen, wurde ein zweiter Reaktionspuffer vorbereitet, der kein CaCl2, dafür EGTA in einer Konzentration von 5 mM enthielt.
Nach der Zubereitung der Puffer wurde radioaktiv markiertes [?-32P]-ATP (4500 Ci/mmol) in
einer Endkonzentration von 0.03 µM dazugegeben. Daraus resultierte eine spezifische Aktivität
im Ansatz von 5.8 * 105 dpm/pmol ATP. Die zu testenden Proteine (GST-CDPK: je 0.4 µg,
CT66: je 5 µg und GST: je 1.1 µg) wurden in 1.5 ml Reaktionsgefässen vorgelegt und die Reaktionen durch Zugabe des jeweiligen Puffers gestartet.
Nach der vorgesehenen Inkubationszeit von 5, 25 oder 125 min bei 25 °C wurden die Reaktionen durch Zugabe von je 20 µl 2x SDS-Probenpuffer abgestoppt und die Proteine während 5
min bei 95 °C denaturiert. Anschliessend wurden je 30 µl der Proben über ein TRICIN-SDSPolyacrylamidgel (16.5 % w/v, Dicke 1.5 mm, nach Schägger und von Jagow, 1987) bei 80 V
aufgetrennt. Danach wurde das Gel wie oben beschrieben gefärbt, getrocknet und autoradiographiert.
2. Material und Methoden
Seite 25
2.4.5 Aktivitätsbestimmung der Plasmamembran-H+-ATPase
Vorinkubation der Plasmamembran-Vesikel zur Phosphorylierung der H+-ATPase:
Die in diesem Versuch verwendeten Plasmamembran-Vesikel wurden aus Blattgewebe von
Lycopersicon esculentum extrahiert und zur Verfügung gestellt von A. Schaller, ETH Zürich.
Sie enthielten 0.75 mg Gesamtprotein/ml Vesikelsuspension. Alle Lösungen wurden mit ultrareinem Wasser (Millipore® Filtrationsanlage) unter Verwendung steriler Plastikgefässe angesetzt. In 7.5 µl einer Pufferlösung, die 35 mM MES/Tris pH 7.5, 10 mM MgCl2, 3 mM DTT,
50 µM ATP, 1 mM EGTA, 1.1 mM CaCl2 und 330 mM Sucrose enthielt, wurden 6.1 µg GSTCDPK (in 50 mM Tris/HCl pH 8.0) gegeben. Anschliessend wurde 1 µl PlasmamembranVesikel-Suspension zugegeben und der Ansatz mit einem Totalvolumen von 20 µl während 30
min bei 25 °C vorinkubiert. Parallel dazu wurde ein analoger Ansatz verwendet, der anstelle
der GST-CDPK lediglich 50 mM Tris/HCl pH 8.0 gleichen Volumens enthielt.
Vorbereitung der Messpuffer:
Gleichzeitig zu den Vorinkubationen der Plasmamembran-Vesikel wurden zwei Messpuffer
mit einem Totalvolumen von je 90 µl vorbereitet und auf 38 °C erwärmt: 36 mM MES/Tris pH
6.0 oder 7.3 (je nach Versuch), 56 mM KCl, 5 mM MgSO4, 1 mM NaMoO4, 50 mM NaNO3,
0.02 % (v/v) Triton X-100, 3 mM ATP und fakultativ 1 mM NaVO4. Die angegebenen Konzentrationen beziehen sich auf das Endvolumen von 100 µl bei der nachfolgenden Aktivitätsmessung.
Aktivitätsmessung:
Durch Zugabe von 10 µl des Vorinkubations-Ansatzes (mit den Plasmamembran-Vesikeln)
zum Messpuffer wurde die Aktivätsmessung gestartet. Nach einer Inkubationszeit von 3, 6 oder
9 min bei 38 °C wurde die Menge des freien Phosphats bestimmt (Lanzetta et al., 1979). Den
Reaktionsansätzen wurde je 1 ml eines Phosphatreagenzes (bestehend aus 0.034 % (w/v) Malachitgrün, 1 % (w/v) Ammoniumheptamolybdat, 0.04 % (v/v) Tergitol NP-10 und 1 M HCl)
zugesetzt, bevor sie während 1 min bei 38 °C inkubiert wurden. Anschliessend wurde die Reaktion durch Zugabe von 200 µl 34 % (w/v) Natriumcitrat gestoppt und die Reaktionsgefässe
bei Raumtemperatur im Dunkeln während 2 h aufbewahrt, bevor die Extinktionen bei 660 nm
mit dem Spektrophotometer bestimmt wurden.
Die Konzentration des jeweils entstandenen freien Phosphats wurde anhand einer Standardkurve berechnet, die mit einer KH2PO4-Konzentrationsreihe (1 bis 22 nmol/100 µl in 2 nmol-
2. Material und Methoden
Seite 26
Schritten) erstellt wurde (siehe Abschnitt 6.2). Alle Einzelmessungen wurden dreifach ausgeführt.
2.4.6 Amplifizierung der cDNAs CDPKwt und CDPKmut mittels PCR
Mittels der PCR (polymerase chain reaction) wurden zwei verschiedene LeCPK1-cDNAs amplifiziert: CDPKwt und CDPKmut.
CDPKwt codiert für die Wildtyp-LeCPK1, nachfolgend CDPKwt genannt. Für ihre Herstellung
wurde das Primerpaar 5PKwt (5‘-Primer) und 3PKwt (3'-Primer) verwendet. Beide Primer umfassten eine XbaI-Restriktions-Schnittstelle, um die Klonierung des PCR-Produktes zu erleichtern. Es wurden 10 Amplifikationszyklen (94 °C / 20 s, 52 °C / 30 s, 72 °C / 90 s), anschliessend 20 Zyklen (94 °C / 20 s, 52 °C / 30 s, 72 °C / 90 s + 5 s pro Zyklus) auf einer PCRMaschine (Perkin Elmer Cetus Thermal Cycler) durchgeführt.
CDPKmut codiert für eine LeCPK1-Mutante, nachfolgend CDPKmut genannt, bei der eine
essentielle Aminosäure des Myristoylierungs-Konsensusmotivs ausgetauscht worden ist. Es
handelt sich dabei um eine Gly2Ala-Substitution, die durch Verwendung eines entsprechend
angepassten Primers erreicht wurde. Für die Amplifikation dieser cDNA wurde das Primerpaar
5Pkmut (5'-Primer) und 3PKwt (3'-Primer) verwendet. Damit bei der PCR-Reaktion in der
Mehrzahl mutierte cDNAs amplifiziert wurden, wurden zuerst sechs Zyklen nur mit dem
5PKmut-Primer durchgeführt, um die Ausgangsmenge des erwünschten Templats für die nachfolgenden Amplifizierungsschritte zu erhöhen. Anschliessend wurden wie oben 10 Zyklen (94
°C / 20 s, 52 °C / 30 s, 72 °C / 90 s), dann 20 Zyklen (94 °C / 20 s, 52 °C / 30 s, 72 °C / 90 s +
5 s pro Zyklus) durchgeführt.
Beide Reaktionen fanden in einem Gesamtvolumen von 100 µl statt, unter Verwendung von je
300 nM Primer-Oligonukleotiden (Microsynth), 300 ng pGEX-G-CDPKwt Templat-cDNA
(Stalder, 2000), 2.5 U Pwo DNA-Polymerase, 200 µM dNTPs, 2 mM MgSO4 und 10 µl Reaktionspuffer (10x). Die Ansätze wurden mit ddH2O auf 100 µl Gesamtvolumen ergänzt und mit
zwei Tropfen Öl überschichtet.
Nach der Reaktion wurde ein Aliquot der PCR-Produkte auf einem 0.8 % (w/v) Agarosegel
analysiert. Dann wurde die cDNA durch Phenol- und Phenol-Chloroform (1:1)-Extraktionen
und anschliessende Ethanol-Präzipitation aus dem Reaktionsansatz gereinigt.
2. Material und Methoden
Seite 27
Für die Amplifizierung der cDNAs verwendete Primer:
5PKwt:
5‘-CCTCTAGAATGGGTGGTTGTTTTAGCAA-3‘
5PKmut: 5‘-CCTCTAGAATGGCTGGTTGTTTTAGCAAGAAGT-3‘
3PKwt:
5‘-GGTCTAGAGGGAAAAGCTTTTGTTGTGGTTGT-3‘
2.4.7 Ligation der amplifizierten cDNAs in die Vektoren pBluescript SK(-) und pcl60
Um die beiden cDNAs in die entsprechenden Vektoren ligieren zu können, wurden sowohl die
beiden cDNAs wie auch die Vektor-DNAs mit dem Restriktionsenzym XbaI restringiert.
12 µg des Vektors pBluescript SK(-) (Stratagene) wurden in einem 100 µl-Ansatz mit 60 U
XbaI und 100 µg/ml BSA (MBI Fermentas) in einem entsprechenden Puffer während 60 min
bei 37 °C restringiert und dann während 10 min bei 37 °C mit 2 U CIAP (Calf Intestine Alkaline Phosphatase, MBI Fermentas) dephosphoryliert. Schliesslich wurden die Enzyme während
10 min bei 65 °C hitzeinaktiviert und dann die geschnittene Vektor-DNA mit Phenol- und Phenol-Chloroform (1:1)-Extraktionen und anschliessender Ethanol-Präzipitation gereinigt. Um
eine vollständige Restriktion zu erreichen, wurden diese Schritte zweimal wiederholt. Auf gleiche Weise wurden 7 µg des Vektors pcl60 vorbereitet.
Die cDNAs (je 4.5 µg) wurden in je einem 40 µl-Ansatz mit 24 U XbaI und 100 µg/ml BSA
während 60 min bei 37 °C inkubiert. Wiederum wurden die Reaktionen durch Hitzeinaktivierung bei 65 °C gestoppt und die geschnittenen cDNAs mittels Phenol- und Phenol-Chloroform
(1:1)-Extraktionen und anschliessender Ethanol-Präzipitation gereinigt. Die gewünschten
cDNA-Fragmente wurden anschliessend auf einem 0.8 % (w/v) Agarosegel aufgetrennt, im
UV-Licht als entsprechende Banden ausgeschnitten und mit dem "Prep-A-Gene® DNA Purification Kit" (Bio-Rad) gemäss Protokoll des Herstellers aus dem Gel eluiert.
Je 150 ng der restringierten cDNA (zukünftige Insert-cDNA) wurden dann mit je 100 ng Vektor-DNA in einem 10 µl-Ligationsansatz mit 1 U T4 DNA-Ligase über Nacht bei 16 °C inkubiert. Nach Hitzeinaktiverung während 10 min bei 65 °C wurden die Ligationsprodukte mit
Ethanol gefällt, getrocknet und in je 2 µl ddH2O aufgenommen.
2. Material und Methoden
Seite 28
2.4.8 Transformation von kompetenten E. coli-Zellen
Für die Transformation wurden die vier Ligationsprodukte zu 200 µl kompetenten, auf Eis aufgetauten E. coli-Zellen (TOP10', Invitrogen One Shot®) gegeben und 5 min auf Eis, 30 s im 42
°C-Wasserbad und wieder 1 min auf Eis inkubiert. Die Ansätze wurden mit 250 µl SOCMedium (Invitrogen) ergänzt und während 1 h bei 37 °C mit 150 rpm geschüttelt. Je 125 µl der
Ansätze wurden dann auf LBAmp Agar-Petrischalen ausplattiert und über Nacht bei 37 °C inkubiert.
2.4.9 Isolierung von Plasmid-DNA (Mini Prep) aus E. coli
Die Plasmid-DNA wurde nach dem Prinzip der alkalischen Lyse isoliert (Birnboim und Doly,
1979). Mit einzelnen, auf LBAmp Agar-Petrischalen gewachsenen Kolonien wurden je 2 ml
LBAmp-Flüssigkulturen inokuliert. Die Kulturen wurden erneut über Nacht bei 37 °C und 220
rpm auf dem Schüttler inkubiert.
Am darauffolgenden Tag wurden jeweils 1.5 ml der 2 ml-Kulturen bei 14'000 rpm während 2
min in einer Eppendorftischzentrifuge abzentrifugiert, der Überstand verworfen und das Pellet
in 100 µl Mini Prep-Puffer resuspendiert. Nach Zugabe von 150 µl 0.2 N NaOH und 1 % (w/v)
SDS wurde die Suspension während 5 min auf Eis inkubiert, dann mit 150 µl 3 M Kaliumacetat
versehen und für weitere 5 min auf Eis gestellt. Durch Zentrifugation (5 min, 14'000 rpm) wurden Lipide, Proteine und chromosomale DNA sedimentiert und der Überstand in ein neues 1.5
ml Reaktionsgefäss mit 800 µl vorgelegtem Ethanol transferiert.
Es folgten eine Inkubation auf Eis während 15 min und eine weitere Zentrifugation (15 min,
14'000 rpm), bevor die auf diese Weise präzipitierte Plasmid-DNA in 200 µl TE-Puffer, enthaltend 1 µl pankreatische RNAse (10 mg/ml), aufgenommen und anschliessend während 30
min bei 37 °C inkubiert wurde. Dann führte man Extraktionen mit Phenol und mit Phenol/Chloroform (1:1) durch, gefolgt von einer Ethanolfällung der Plasmid-DNA. Das Präzipitat
wurde in 50 µl H2O aufgenommen und bei –20 °C gelagert.
2. Material und Methoden
Seite 29
2.4.10 Analyse der Ligationsprodukte durch Restriktion der Plasmid-DNA
Um zu überprüfen, ob die Plasmide ein DNA-Insert enthielten und ob dieses in gewünschter
Orientierung relativ zum T7 bzw. 35S-Promotor in die Vektor-DNA ligiert worden war, wurden ca. 400 ng der isolierten Plasmid-DNA in einem 20 µl-Ansatz mit 5 U EcoRI während 1 h
bei 37 °C restringiert. Nachdem die Reaktion durch Hitzeinaktivierung während 10 min bei 65
°C gestoppt worden war, wurden die Restriktionsprodukte mittels eines 0.8 % (w/v) Agarosegels aufgetrennt und analysiert.
2.4.11 DNA-Sequenzanalyse
Die DNA-Sequenzierung der Konstrukte erfolgte nach der von Sanger et al. (1977) beschriebenen Kettenabbruchmethode unter Einsatz fluoreszenzmarkierter Dideoxynukleotide. In der
PCR verwendete man in einem Gesamtvolumen von 10 µl 1.6 µl Primer (1.6 pmol T7- sowie
konstruktspezifische Primer, Microsynth), 2 µl Templat-DNA (ca. 250 ng Plasmid-DNA), 4 µl
Reaktionsmix inkl. Taq DNA-Polymerase und Reaktionspuffer (Perkin Elmer) und 2.4 µl
ddH2O. Es wurden 25 Amplifikationszyklen (95 °C / 30 s, 50 °C / 15 s, 60 °C / 240 s) durchgeführt. Anschliessend wurden die Reaktionsprodukte mit Ethanol gefällt, in 4 µl Ladepuffer aufgenommen und während 2 min bei 95 °C denaturiert.
Die Trennung der Oligonukleotidstränge erfolgte über ein 5% (w/v) Polyacrylamid-Gel in Gegenwart von 8 M Harnstoff und mit 1x TBE als Laufpuffer. Die Elektrophorese dauerte bei
2500 V und 38 W 17 Stunden (ABI 373 DNA Sequencer, Perkin Elmer). Die erhaltenen Daten
wurden mit Hilfe des Software-Paketes der University of Wisconsin Genetics Computer Group
(GCG) analysiert.
2.4.12 Amplifizierung und Isolierung der Konstrukte in/aus E. coli (Midi Prep)
Die Plasmid-DNA jeweils eines Klones wurde in E. coli amplifiziert und durch "Midi Prep"
gereinigt. Dazu wurde mit den entsprechenden 2 ml-Vorkulturen jeweils eine grössere 200 ml
LBAmp-Flüssigkultur in einem 1 Liter-Erlenmeyerkolben inokuliert. Die Kulturen wurden über
Nacht bei 37 °C und 220 rpm auf dem Schüttler inkubiert. Anschliessend konnte die PlasmidDNA durch Verwendung des "Eppendorf Perfectprep® Plasmid Midi-Kits" gemäss Protokoll
2. Material und Methoden
Seite 30
des Herstellers extrahiert und in 200 µl TE-Puffer aufgenommen werden. Zur Bestimmung der
DNA-Konzentration wurde die Extinktion einer 200-fachen Verdünnung bei 260 nm im Spektrophotometer gemessen.
2.4.13 In vitro-Transkription/Translation und Myristoylierung der LeCPK1
Zunächst wurden jeweils 8 µg Vektor-DNA (pSK-CDPKwt oder pSK-CDPKmut) in einem 100
µl-Ansatz mit 50 U NotI während 1 h bei 37 °C inkubiert und dadurch 3'-terminal des cDNAInserts linearisiert. Danach wurde die Reaktion durch Hitzeinaktivierung während 10 min bei
65 °C gestoppt. Nach darauffolgenden Phenol- und Phenol-Chloroform (1:1)-Extraktionen und
einer Ethanolfällung wurden die linearisierten Vektor-DNAs in je 12 µl nukleasefreiem ddH2O
aufgenommen.
Die in vitro-Transkription/Translation vom T7-Promotor des pSK-Vektors aus erfolgte in einem TNT® gekoppelten Weizenkeimextrakt-System (Promega) nach Angaben des Herstellers.
Für die Transkription/Translation wurden Ansätze mit einem Totalvolumen von jeweils 25 µl
in 1.5 ml Reaktionsgefässen verwendet. Sie enthielten je 0.6 µg linearisierte pSK-CDPKwtcDNA oder 1 µg pSK-CDPKmut-cDNA, 12.5 µl Weizenkeimextrakt, 1 µl Reaktionspuffer, 20
U RNAsin (Promega), wahlweise 20 µM Aminosäuren-Mix (ohne Methionin) oder 20 µM
Aminosäuren-Mix (komplett), wahlweise 40 µM [9,10-3H]-Myristinsäure (50 Ci/mmol, Moravek Biochemicals) oder 10 µM [35S]-Methionin (1000 Ci/mmol, Hartmann Analytic) und 0.5 µl
T7 RNA-Polymerase.
Die [9,10-3H]-Myristinsäure, welche als ethanolische Lösung geliefert worden war, trocknete
man zuerst in der Vakuumzentrifuge und resuspendierte sie dann während 15 min im Ultraschallbad in 9 µl nukleasefreiem ddH2O. Für die Positivkontrolle wurde anstelle der LeCPK1cDNAs 1.5 µg einer für Luciferase codierenden cDNA (Promega) eingesetzt.
Nach Zugabe der RNA-Polymerase als Initiator der Reaktionen wurden die Ansätze während
90 min bei 30 C° inkubiert. Dann wurden die Reaktionen durch Zugabe von je 25 µl 2x SDSProbenpuffer abgestoppt und die Proteine während 5 min bei 95 °C denaturiert. Anschliessend
wurden je 5 µl oder 10 µl der Proben auf ein SDS-Polyarcrylamidgel (10 %, Dicke 1.5 mm)
geladen und bei 125 V aufgetrennt.
Die Proteinbanden wurden danach während 30 min in Gelfärbelösung (basierend auf Coomassie Brilliant Blue R 250) gefärbt und das Gel während 30 min in Gelfixierlösung schüttelnd
2. Material und Methoden
Seite 31
entfärbt. Anschliessend inkubierte man das Gel während 60 min in 100 ml EN3HANCE(™)Lösung (DuPont NEN). Nach einer zweistündigen Inkubation in ddH2O wurde das Gel während 2 h bei 80 °C im Geltrockner getrocknet. Die Fluorographie erfolgte während 60 h bei –80
°C (mit Reflektorfolie) auf Kodak X-OMAT AR-Röntgenfilm. Anschliessend wurde der Film
maschinell entwickelt.
2.4.14 Transformation von Zwiebelepidermiszellen und transiente Expression
der Fusionsproteine CDPKwt-EGFP und CDPKmut-EGFP
Die Transformation von Zwiebelepidermiszellen durch Beschuss mit Goldpartikeln wurde im
Wesentlichen wie von Scott et al. beschrieben durchgeführt (Scott et al., 1999). Von den Unterblättern ("Schalen") einer Zwiebel (Allium cepa) wurden ca. 1 cm2 grosse Stücke der Epidermis der Blattinnenseite mit Skalpell und Pinzette abgezogen und auf MS-Agar in Petrischalen flach ausgelegt. Anschliessend wurden die drei zu transformierenden cDNAs (CDPKwtEGFP, CDPKmut-EGFP und EGFP als Kontrolle), die alle in das Plasmid pcl60 unter Kontrolle des 35S-Promotors ligiert worden waren, an Goldpartikel gebunden.
Diese wurden wie folgt vorbereitet: In einem 1.5 ml Reaktionsgefäss wurden 50 mg Goldpartikel (Grösse: 1.5 bis 3 µm, Aldrich) in 1 ml 100% EtOH p.a. aufgenommen und am Sonicator
(W-380, Heat Systems, Ultrasonics) während 30 s mit Ultraschall resuspendiert. Danach wurden die Partikel bei 14'000 rpm während 30 s in einer Eppendorftischzentrifuge abzentrifugiert,
der Überstand verworfen und das Pellet erneut in 1 ml 100% EtOH p.a. aufgenommen. Nach
fünfmaliger Wiederholung dieser Waschschritte wurden die Partikel an der Luft getrocknet, in
1 ml 50 % Glycerol (v/v) aufgenommen und während 30 s mit Ultraschall resuspendiert. Zum
Schluss lag eine gebrauchsfertige Goldpartikelsupension in einer Konzentration von 50 µg/µl
vor.
Für jedes Konstrukt wurden 30 µl dieser Suspension in einem 1.5 ml Reaktionsgefäss mit 10 µl
Plasmid-DNA (0.4 µg/µl) vermengt, bevor durch Zugabe von 30 µl 2.5 M CaCl2 und 12 µl 0.1
M Spermidin und heftiges Mischen während 3 min die cDNAs an die Goldpartikel gebunden
wurden. Durch schrittweise Zugabe von insgesamt 300 µl 100% EtOH p.a. und einer Inkubation von 30 min bei –20 °C wurde die DNA präzipitiert. Kurz vor der Transformation wurden
die Partikel sedimentiert (14'000 rpm während 30 s in einer Eppendorftischzentrifuge), der ethanolische Überstand abgenommen, die Goldpartikel in 25 µl ddH2O aufgenommen und während ca. 20 s mit Ultraschall resuspendiert.
2. Material und Methoden
Seite 32
Die Transformation der Zwiebelepidermiszellen erfolgte mittels der Mikroprojektiltechnik. Mit
Hilfe einer Particle Inflow Gun (Eigenbau der Gruppe Biotechnologie der Pflanzen, ETH Zürich) wurden die auf MS-Agar ausgelegten Epidermisstücke mit 7 µl (4 µg) Goldpartikelsuspension beschossen. Durch einen Heliumdruckstoss von 9 bar wurden die DNAbeladenenen Goldpartikel in der auf –0.8 bar evakuierten Kammer beschleunigt [Anmerkung:
Die Loch- bzw. Tragegitter für die Petrischalen befanden sich auf Position 3 bzw. 4 (Numerierung der Gitterebenen von oben)]. Zur Expression der transferierten cDNAs wurden die Petrischalen nach der Transformation für mind. 24 h in eine Klimakammer (23 °C; Lichtzyklus 16 h
Licht (1 µE * s-1 * m-2) und 8 h Dunkel) gebracht.
Anschliessend wurde jeweils ein Epidermisstück mit einem Tropfen ddH2O auf einen Objektträger gegeben, das Präparat mit einem Deckglas fixiert und sofort mittels eines spektralen,
konfokalen Laser-Scanning Mikroskopes (Leica TCS SP mit Leica DM IRBE) untersucht. Für
die Fluoreszenz-Anregung und konfokale Abrasterung wurde ein ArKr-Laser bei 488 nm verwendet. Emittiertes Licht wurde im Bereich von 500 bis 520 nm detektiert. Für 50 bis 100fache Vergrösserungen wurden Luft-Glas-Objektive, für 200 bis 1000-fache Vergrösserungen
Ölimmersionsobjektive verwendet. Die Bildverarbeitung erfolgte mit der Software Leica TCS
NT, Version 1998.
2.4.15 Transformation von Lycopersicon peruvianum-Suspensionskulturzellen und
transiente Expression der Fusionsproteine CDPKwt-EGFP und CDPKmut-EGFP
Jeweils 4 bis 5 ml einer sieben Tage alten Zellsuspensionskultur von Lycopersicon peruvianum
wurden gleichmässig auf Petrischalen (Durchmesser 5 cm) mit Plasmolyse-Agar pipettiert.
Anschliessend wurden die drei zu transformierenden Konstrukte an Goldpartikel gebunden
(siehe Abschnitt 2.4.14). Die Transformation der Lycopersicon peruvianum-Zellen erfolgte
wiederum mittels der Particle Inflow Gun, in welcher eine Petrischale mit der auf PlasmolyseMedium verteilten Zellsuspension durch einen Heliumdruckstoss von 6 bar in einer auf –0.9
bar evakuierten Kammer mit 7 µl (4 µg) der obigen, DNA-beladenenen Goldpartikelsuspension
beschossen wurde. [Anmerkung: Die Loch- bzw. Tragegitter für die Petrischalen befanden sich
auf Position 2 bzw. 4 (Numerierung der Gitterebenen von oben)].
Zur Expression der transferierten cDNAs wurden die Petrischalen nach der Transformation für
mind. 24 h in eine Klimakammer (23 °C; Lichtzyklus 16 h Licht (1 µE * s-1 * m-2) und 8 h
Dunkel) gebracht.
2. Material und Methoden
Seite 33
Anschliessend wurden die Zellen jeweils einer Petrischale mit einem sterilen Spatel in ein 2.0
ml Reaktionsgefäss überführt, dort mit 1.5 ml Nover-Medium resuspendiert und dann im Überkopfschüttler während 30 min bei Raumtemperatur inkubiert. Danach wurden jeweils 250 µl
Zellsuspension mit einer Pipette auf einen Objektträger gegeben, mit einem Deckglas fixiert
und am spektralen, konfokalen Laser-Scanning Mikroskop untersucht (siehe Abschnitt 2.4.14).
2.4.16 Titration einer GST-CDPK-Lösung mit CaCl2 unter paralleler Aufnahme des
Fluoreszenz-Spektrums
Ein Milliliter einer 0.5 µM (0.045 mg/ml) GST-CDPK-Lösung (in 50 mM HEPES pH 7.5)
wurde in eine Quarz-Küvette gegeben. Mit einem Fluoreszenz-Spektrophotometer (Kontron
SFM 25, Rotkreuz) wurde das Emissionsspektrum nach Anregung bei 280 nm aufgenommen.
Dabei wurde der Photomultiplier des Spektrometers mit einer Spannung von 430 V betrieben.
Es wurden schrittweise steigende Konzentrationen von CaCl2 (in 50 mM HEPES pH 7.5) zugegeben. Nach jedem Titrationsschritt wurde erneut ein Fluoreszenzspektrum aufgenommen. Die
CaCl2-Lösungen lagen in Konzentrationen von 0.1 mM bis 1 M vor und wurden in 2 µlSchritten zugesetzt. Die gewonnenen Daten wurden mit den Programmen Excel 97 (Microsoft)
und SigmaPlot 6.0 (SPSS Inc.) ausgewertet.
3. Resultate
Seite 34
III. RESULTATE
3.1 Expression und Aufreinigung der GST-Fusionsproteine GST-CT56 und
GST-CT66 sowie des GST-Proteines selbst
Um zu untersuchen, ob die Plasmamembran-H+-ATPase ein Substrat der LeCPK1 ist, wurden
zuerst zwei C-terminale Fragmente der Protonenpumpe heterolog exprimiert und gereinigt.
Das Reinigungsprinzip der Glutathion Sepharose-Affinitätschromatographie beruht auf der
Fähigkeit des GST-Anteils des Fusionsproteins, selektiv an die Glutathion Sepharose-Matrix zu
binden.
Dieses Prinzip wurde ausgenutzt, um die LeCPK1 und zwei C-terminale Fragmente der Plasmamembran-H+-ATPase PMA2 von Nicotiana plumbaginifolia als GST-Fusionsproteine zu
reinigen. Bei den zwei C-terminalen Teilpeptiden handelt es sich um GST-CT56, ein GSTFusionspeptid, das aus den 56 letzten C-terminalen Aminosäuren der Plasmamembran-H+ATPase besteht, und GST-CT66, das die 66 letzten C-terminalen Aminosäuren der Plasmamembran-H+-ATPase umfasst. Zusätzlich wurde das GST-Protein (die Glutathion STransferase) selbst in E. coli exprimiert und gereinigt.
Wie die SDS-PAGE-Analyse ergab, gelang die Aufreinigung der GST-Fusionsproteine mit
hoher Spezifität. Bei den Fusionsproteinen GST-CT56 (Abb. 5) und GST-CT66 (Abb. 6) sind
trotz der bereits während der Lyse eingesetzten Proteasehemmstoffe in den Eluaten kleinere
Degradationsprodukte zu finden, wobei das kleinste auf dem Gel sichtbare Abbauprodukt
wahrscheinlich der Glutathion S-Transferase selbst (Abb. 7) entspricht.
3. Resultate
Seite 35
M
R
D
E
97.4 kDa
66.2 kDa
45.0 kDa
GSTCT56
31.0 kDa
Abb. 5: Reinigung des GST-CT56-Fusionsproteines
durch Glutathion Sepharose-Affinititätschromatographie.
R: Rohextrakt (20 µl von 24 ml Gesamtvolumen).
D: Durchfluss (20 µl von 10 ml Gesamtvolumen).
E: Vereinigte Eluatfraktionen (3 µl von 3 ml Gesamtvolumen).
Das Fusionsprotein besitzt eine errechnete Grösse von 32.3 kDa.
SDS-PAGE-Gel (10%), Coomassie Brilliant Blue-gefärbt,
Marker: low molecular weight standards (Bio-Rad).
M
E1
E2
E3
E4
E5
97.4 kDa
66.2 kDa
45.0 kDa
GSTCT66
31.0 kDa
14.4 kDa
Abb. 6: Reinigung des GST-CT66-Fusionsproteines
durch Glutathion Sepharose-Affinititätschromatographie.
Gezeigt sind die fünf ersten mit reduziertem Glutathion
eluierten Fraktionen (Spuren E1 bis E5). Pro Spur
wurden 15 µl von 1 ml Fraktionsvolumen aufgetragen.
Das Fusionsprotein besitzt eine errechnete Grösse von 33.3 kDa.
SDS-PAGE-Gel (10%), Coomassie Brilliant Blue-gefärbt,
Marker: low molecular weight standards (Bio-Rad).
3. Resultate
Seite 36
M
E1
E2
E3
E4
E5
97.4 kDa
66.2 kDa
45.0 kDa
31.0 kDa
GST
14.4 kDa
Abb. 7: Reinigung der Glutathion S-Transferase (GST)
durch Glutathion Sepharose-Affinititätschromatographie.
Gezeigt sind die fünf ersten mit reduziertem Glutathion
eluierten Fraktionen (Spuren E1 bis E5). Pro Spur wurden
15 µl von 500 µl Fraktionsvolumen aufgetragen.
Das GST-Protein besitzt eine errechnete Grösse von 26.1 kDa.
SDS-PAGE-Gel (10%), Coomassie Brilliant Blue-gefärbt,
Marker: low molecular weight standards (Bio-Rad).
3. Resultate
Seite 37
3.2 In vitro-Phosphorylierung der Plasmamembran-H+-ATPase
Im folgenden in vitro-Phosphorylierungs-Experiment wurde untersucht, ob der C-Terminus der
Plasmamembran-H+-ATPase ein Substrat der LeCPK1 ist. Dazu wurden die gereinigten Fusionsproteine der C-Termini (GST-CT56 und GST-CT66) mit der gereinigten GST-CDPK in
Gegenwart von [?-32P]-ATP inkubiert. Die Reaktionsprodukte wurden mittels SDS-PAGE aufgetrennt (Abb. 8a) und durch Autoradiographie analysiert (Abb. 8b).
GST-CT66 wurde zeitabhängig phosphoryliert (Abb. 8b, Spuren 1-3). Daneben war auch eine
zeitabhängige Autophosphorylierung der GST-CDPK zu beobachten. Sowohl die Phosphorylierung in trans als auch die Autophosphorylierung erwiesen sich als Ca2+-abhängig (Abb. 8b,
Spur 4). Es fällt auf, dass die Autophosphorylierung erheblich stärker ist als die Phosphorylierung von GST-CT66. Eine mögliche Ursache hierfür ist, dass der Km-Wert vieler CDPKs für
ATP im Falle der Phosphorylierung in trans erheblich höher ist als für die Autophosphorylierung (Chaudhuri et al., 1999). Die Phosphorylierung des C-Terminus GST-CT66 fand also
möglicherweise unter suboptimalen Bedingungen statt. Weiterhin wäre es denkbar, dass mehrere Ser/Thr-Reste der GST-CDPK autophosphoryliert werden, während der C-Terminus lediglich eine phosphorylierbare Aminosäure enthält. Darüber hinaus mag die Autophosphorylierung als intramolekulare Reaktion gegenüber einer intermolekularen Reaktion begünstigt sein.
Eine Ca2+-abhängige Phosphorylierung der Glutathion S-Transferase (GST) selbst (Abb. 8b,
Spuren 7 und 8) ist nachweisbar, aber deutlich schwächer als die Phosphorylierung von GSTCT66 (Abb. 8b, Spuren 3 und 4). Offensichtlich ist also CT66 ein in vitro-Substrat der GSTCDPK.
Zwischen den für GST-CT56 und GST-CT66 enthaltenen Resultaten waren keine Unterschiede
festzustellen (das GST-CT56-Ergebnis wird deshalb hier nicht gezeigt). Dies lässt darauf
schliessen, dass sich an den zehn zusätzlichen Aminosäuren des GST-CT66 keine zusätzliche
Phosphorylierungsstelle befindet.
3. Resultate
Seite 38
M
1
2
3
4
5
6
7
8
1 min
5 min
25 min
–Ca2+
–GSTCT66
–GSTCDPK
–GSTCT66
+GST
–GST-CT66
+GST
-Ca2+
GSTCDPK
97.4 kDa
66.2 kDa
45.0 kDa
GSTCT66
31.0 kDa
GST
14.4 kDa
A
GSTCDPK
97.4 kDa
66.2 kDa
45.0 kDa
GSTCT66
GST
31.0 kDa
B
Abb. 8: Phosphorylierung des C-Terminus GST-CT66 der Plasmamembran-H+-ATPase durch die GST-CDPK.
A: SDS-PAGE-Gel (10%), Coomassie Brilliant Blue-gefärbt, Marker: low molecular weight standards (Bio-Rad).
B: Autoradiographie des unter A gezeigten Gels.
Spuren 1-3: Die aufgetragenen Proben enthalten die GST-CDPK (86.9 kDa) und den C-Terminus GST-CT66
(33.3 kDa), die in einem Ca2+-haltigen Puffer während 1, 5 oder 25 min inkubiert wurden.
Spur 4:
Ansatz wie 3, aber ohne Ca2+.
Spur 5:
Ansatz wie 3, aber ohne C-Terminus GST-CT66.
Spur 6:
Ansatz wie 3, aber ohne GST-CDPK.
Spur 7:
Ansatz wie 3, aber anstelle des C-Terminus GST-CT66 wurde das GST-Protein selbst (26.1 kDa)
eingesetzt.
Spur 8:
Ansatz wie 7, aber ohne Ca2+.
3. Resultate
Seite 39
3.3 Phosphorylierung des vom GST-Peptid abgetrennten C-Terminus der
Plasmamembran-H+-ATPase
Um sicherzustellen, dass die in Abschnitt 3.2 festgestellte Phosphorylierung von GST-CT66
durch die GST-CDPK tatsächlich am C-Terminus der H+-ATPase und nicht etwa am GSTPeptid des Fusionsproteines stattfindet, wurde der GST-Anteil des Fusionsproteines proteolytisch mit Thrombin abgetrennt. Anschliessend wurden die Phosphorylierungsreaktionen wie in
Abschnitt 3.2 durchgeführt, die Reaktionsprodukte mittels TRICIN-SDS-PAGE aufgetrennt
(Abb. 9a) und durch Autoradiographie analysiert (Abb. 9b).
Der C-Terminus CT66 (26 kDa) wurde zeitabhängig (Abb. 9, Spuren 1 bis 3) und Ca2+abhängig (Abb. 9, Spur 4) phosphoryliert, nicht aber das von ihm abgetrennte GST-Peptid (7.3
kDa). Die Phosphorylierung durch die GST-CDPK findet also am C-Terminus CT66 selbst
statt, und nicht etwa am GST-Anteil des Fusionsproteins. Bei Einsatz von GST als Substrat
ohne vorherige Spaltung mit Thrombin ist allerdings eine gewisse Phosphorylierung zu beobachten (Abb. 9, Spuren 7 und 8, siehe auch Abb. 7, Spuren 7 und 8). Das legt die Vermutung
nahe, dass einige vom Polylinker des Expressionsplasmids codierte Aminosäuren (C-terminal
der Thrombin-Schnittstelle) eine Phosphorylierungsstelle für die LeCPK1 darstellen.
3. Resultate
Seite 40
M
1
2
3
4
5
6
7
8
5 min
25 min
125 min
–Ca2+
–CT66
–GSTCDPK
–CT66
+GST
–CT66
+GST
-Ca2+
GST
26.6 kDa
17.0 kDa
14.4 kDa
CT66
6.5 kDa
A
GSTCDPK
GST
26.6 kDa
17.0 kDa
14.4 kDa
6.5 kDa
CT66
B
Abb. 9: Phosphorylierung des vom GST-Peptid abgetrennten C-Terminus CT66 durch die GST-CDPK.
A: TRICIN-SDS-PAGE-Gel (16.5% w/v), Coomassie Brilliant Blue-gefärbt, Marker: polypeptide standards
(Bio-Rad).
B: Autoradiographie des unter A gezeigten Gels.
Spuren 1-3: Nach Spaltung des C-Terminus GST-CT66 (33.3 kDa) mit Thrombin wurden die Proteine für
5, 25 oder 125 min mit der GST-CDPK (86.9 kDa) inkubiert.
Spur 4:
Ansatz wie 3, aber ohne Ca2+.
Spur 5:
Ansatz wie 3, aber ohne den C-Terminus GST-CT66.
Spur 6:
Ansatz wie 3, aber ohne die GST-CDPK.
Spur 7:
Ansatz wie 3, aber mit GST (26 kDa) anstelle des geschnittenen Fusionsproteines GST-CT66.
Spur 8:
Ansatz wie 7, aber ohne Ca2+.
3. Resultate
Seite 41
3.4 Die Wirkung von Proteinkinase-Inhibitoren auf die Phosphorylierung des
C-Terminus der Plasmamembran-H+-ATPase
Im Anschluss zu der in 3.2 und 3.3 gezeigten Phosphorylierung des C-Terminus GST-CT66 der
Plasmamembran-H+-ATPase durch die GST-CDPK sollte im vorliegenden Experiment der Einfluss von verschiedenen Proteinkinase-Inhibitoren auf diese Phosphorylierung untersucht werden. Folgende Inhibitoren wurden eingesetzt:
Inhibitor
Inhibierte Kinase(n)
Staurosporin
allgemeiner Proteinkinaseinhibitor
allgemeiner Proteinkinaseinhibitor
Ca2+/CaM-Kinasen II
(CaMKII)
Proteinkinase C
K-252a
KN-62
Bisindolmaleimid
Eingesetzte
Spur in
Konzentration Abb. 10
5
4 µM
2 µM
6
5 µM
7
0.2 µM
8
Zusätzlich wurde auch die Wirkung von Fusicoccin auf die Phosphorylierung der Protonenpumpe untersucht. Dieses Toxin aus dem Pilz Fusicoccum amygdalii aktiviert die Plasmamembran-H+-ATPase (Blum et al., 1988; Johansson et al., 1993), indem es den aktiven Komplex
von 14-3-3-Proteinen und dem C-Terminus der H+-ATPase stabilisiert (Oecking et al., 1997;
Jahn et al., 1997). Ausserdem kann die Systemin-induzierte Alkalisierung des Mediums einer
Suspensionskultur von Lycopersicon peruvianum durch Zugabe von Fusicoccin wirksam unterdrückt werden (Schaller und Oecking, 1999).
Das Fusionsprotein GST-CT66 wurde mit der GST-CDPK in Gegenwart von [?-32P]-ATP während 60 min inkubiert. Die Reaktionsprodukte wurden mittels SDS-PAGE aufgetrennt (Abb.
10a) und durch Autoradiographie analysiert (Abb. 10b). Sowohl der C-Terminus GST-CT66 als
auch die GST-CDPK selbst wurden wie im unter 3.2 dargestellten Experiment phosphoryliert,
wobei es sich bei der GST-CDPK um eine Autophosphorylierung handelt (Abb. 10, Spur 3).
Beide Phosphorylierungen erwiesen sich wiederum als Ca2+-abhängig (Abb. 10, Spur 1).
Die Zugabe von 3 µM Fusicoccin hatte keine Auswirkungen auf die Phosphorylierung des CTerminus der H+-ATPase durch die GST-CDPK (Abb. 10, Spur 4). Offenbar beruht die Protonenpumpe-aktivierende Eigenschaft von Fusicoccin nicht auf der direkten Modulation der
Phosphorylierung selbst, sondern auf anderen Mechanismen, wie z.B. der oben beschriebenen
Stabilisierung eines bereits bestehenden, aktiven Komplexes (siehe Abb. 2 auf Seite 6).
3. Resultate
Seite 42
Die allgemeinen Proteinkinase-Inhibitoren Staurosporin und K-252a hingegen schränkten die
Aktivität der GST-CDPK und damit auch die Phosphorylierung des C-Terminus GST-CT66
deutlich ein (Abb. 10, Spuren 5 und 6). Die Verwendung der spezifisch auf andere KinaseTypen wirkenden Inhibitoren KN-62 und Bisindolmaleimid dagegen zeigte keine Auswirkungen auf die Phosphorylierung des C-Terminus (Abb. 10, Spuren 7 und 8).
3. Resultate
Seite 43
1
2
–Ca2+
–GSTCT66
3
4
Positiv- +3 µM
kontrolle Fusicoccin
5
+4 µM
Staurosporin
6
+2µM
K-252a
7
+5 µM
KN-62
8
+200 nM
Bisindolmaleimid
GSTCDPK
97.4 kDa
66.2 kDa
45.0 kDa
GSTCT66
31.0 kDa
A
GSTCDPK
97.4 kDa
66.2 kDa
45.0 kDa
GSTCT66
31.0 kDa
B
Abb. 10: Wirkung von Proteinkinase-Inhibitoren auf die Phosphorylierung des C-Terminus GST-CT66
A: SDS-PAGE-Gel (10%), Coomassie Brilliant Blue-gefärbt, Marker: low molecular weight standards (Bio-Rad).
B: Autoradiographie des unter A gezeigten Gels.
Spur 1
Die GST-CDPK (86.9 kDa) wurde mit dem C-Terminus GST-CT66 (33.3 kDa) in Abwesenheit
von Ca2+ inkubiert (Negativkontrolle).
Spur 2:
Ansatz wie 1, aber mit Ca2+, dafür ohne GST-CT66 (Negativkontrolle).
Spur 3:
Ansatz wie 2, aber mit GST-CT66 (Positivkontrolle).
Spuren 4-8: Die GST-CDPK wurde mit dem C-Terminus GST-CT66 im vollständigen Reaktionspuffer unter
Zusatz der oben angegebenen Proteinkinase-Inhibitoren bzw. Fusicoccin inkubiert.
3. Resultate
Seite 44
3.5 Der Einfluss einer Phosphorylierung der H+-ATPase auf die Aktivität der
Protonenpumpe
In den vorausgehenden Experimenten wurde gezeigt, dass der C-Terminus der Plasmamembran-H+-ATPase durch die GST-CDPK in vitro phosphoryliert wird. In diesem Versuch sollte
nun geprüft werden, ob diese Phosphorylierung auch Konsequenzen auf die Aktivität der Protonenpumpe hat. So wurde der Einfluss der LeCPK1 auf die Aktivität der H+-ATPase in Plasmamembranvesikeln aus Lycopersicon esculentum (zur Verfügung gestellt von A. Schaller)
untersucht, wobei die Hydrolyse von ATP durch Quantifizierung des freigesetzten, anorganischen Phosphats gemessen wurde (Abb. 11 zeigt den Versuchsablauf).
Die Phosphatfreisetzung wurde nach Lanzetta et al. (1979) mittels eines Phosphatreagenzes
bestimmt. Dabei kommt es zu einer Komplexbildung des Phosphats mit dem im Reagenz enthaltenen Malachitgrün und Molybdat, die zu einer Verschiebung des Absorptionsmaximums
führt. Diese wird als Farbveränderung des Ansatzes von gelb nach grün sichtbar. Durch Messung der Extinktion bei 660 nm und Vergleich der erhaltenen Werte mit einer Standardkurve
(siehe Abschnitt 6.2) konnte die Menge des durch ATP-Hydrolyse entstandenen freien Phosphates bestimmt werden.
Die Aktivität der Plasmamembran-H+-ATPase wurde dann wie folgt errechnet:
nmol
pmol
?E ∗ k ∗ 1000
Aktivität in
= pkat =
, wobei k =
(Faktor aus Standardkurve)
?t
?E
s
∆Ε = Relative Extinktion bei 660 nm
Auf diese Weise wird die Gesamtaktivität aller ATP-hydrolysierenden, Phosphat-freisetzenden
Enzyme ermittelt. Die Aktivität der Plasmamembran-H+-ATPase macht hiervon jenen Teil aus,
der sich als durch Orthovanadat hemmbar erweist. Orthovanadat ist ein starker Inhibitor der PTyp-ATPasen, zu denen auch die Plasmamembran-H+-ATPase gehört. Das Anion kompetitiert
dabei mit einem Phosphat des ATPs um die Phosphorylierungsstelle an dem für P-TypATPasen typischen Aspartat-Rest im aktiven Zentrum der ATP-Hydrolyse (Abb. 1 auf Seite 3).
3. Resultate
Seite 45
Die Differenz der gemessenen Aktivitäten in An- und Abwesenheit von Vanadat entspricht
demzufolge der gesamten Aktivität aller P-Typ-ATPasen. Dies entspricht in guter Näherung
der Plasmamembran-H+-ATPase-Aktivität, da die ebenfalls in der Plasmamembran lokalisierten, zu den P-Typ-ATPasen gehörenden Ca2+-ATPasen quantitativ vernachlässigt werden können (Taiz und Zeiger, 1998).
Gesamtaktivität
ohne Vanadat
P-Typ-ATPasen
Berechnete
Aktivitätsdifferenz
Andere ATPhydrolysierende
Enzme
Aktivität
mit Vanadat
Die Plasmamembran-H+-ATPase PMA2 von Nicotiana plumbaginifolia besitzt eine maximale
Aktivität bei pH 6.0 (C. Oecking, Bochum, pers. Mitteilung). Nimmt man ein ähnliches Optimum für die H+-ATPase-Isoformen von Lycopersicon esculentum an und möchte man eine
Inaktivierung der Protonenpumpe durch die LeCPK1 nachweisen, wäre es sinnvoll, die Messung in einem Puffer mit diesem pH-Wert durchzuführen. Vermutet man hingegen eine Aktivierung der H+-ATPase, müssen Bedingungen gewählt werden, bei denen das Enzym noch keine maximale Aktivität besitzt, z.B. bei pH 7.5 (C. Oecking, pers. Mitteilung). Da im vorliegenden Experiment der Einfluss einer Phosphorylierung durch die LeCPK1 auf die Aktivität der
Protonenpumpe unbekannt war, wurden die Versuche sowohl bei pH 6.0 wie auch bei pH 7.5
durchgeführt.
Übereinstimmend mit dem pH-Optimum der Plasmamembran-H+-ATPase PMA2 von Nicotiana plumbaginifolia wurde für die Tomaten-Protonenpumpe bei pH 6.0 gegenüber pH 7.5 eine
dreifach höhere Aktivität gemessen (Abb. 12). Weder bei pH 6.0, noch bei pH 7.5 hatte die
LeCPK1 einen signifikanten Einfluss auf die Aktivität der H+-ATPase (Abb. 12).
3. Resultate
Seite 46
Messpuffer,
±Orthovanadat
Vorinkubations-Puffer, ±GST-CDPK,
Plasmamembran-Vesikel
25 min bei
Raumtemperatur
Vorinkubation:
30 min bei 25 °C
+ ATP
5 min bei 38 °C
Start
Aktivitätsmessung:
9 min bei 38 °C
Stop
+ Phosphatreagenz
60 s bei 38 °C
+ Natriumcitrat
2 h bei Raumtemperatur
Messung der
Extinktion bei
660 nm
Abb. 11: Schematische Darstellung des Versuchsablaufs zur Bestimmung der H+-ATPase-Aktivität
Das Experiment wurde wahlweise mit oder ohne GST-CDPK und Orthovanadat durchgeführt. Die Vorinkubation
der Plasmamembran-Vesikel mit der GST-CDPK erfolgte bei pH 7.5, während die Aktivitätsmessung wahlweise
bei pH 6.0 oder pH 7.5 durchgeführt wurde.
Für eine detaillierte Beschreibung des Versuchsablaufs siehe Abschnitt 2.4.5.
3. Resultate
+
H -ATPaseAktivität
[µmol * min-1 * mg
Membranprotein-1]
Seite 47
0.9
0.8
0.7
mit CDPK
0.6
ohne CDPK
0.5
0.4
0.3
0.2
0.1
0
pH 6.0
pH 7.5
Abb. 12: Einfluss der GST-CDPK auf die Aktivität der Plasmamembran-H+-ATPase aus Blättern von
Lycopersicon esculentum.
Dargestellt sind die Aktivitäten der Plasmamembran-H+-ATPase in Plasmamembran-Vesikeln. Diese ergeben sich
aus der Differenz der gemessenen Aktivitäten in An- und Abwesenheit von Orthovanadat im Messpuffer.
Das Experiment bei pH 7.5 wurde doppelt, jenes bei pH 6.0 dreifach in unabhängigen Versuchen durchgeführt,
deren Ergebnisse gemittelt wurden. Die Fehlerindikatoren geben die prozentualen Abweichungen von diesen Mittelwerten an.
3. Resultate
Seite 48
3.6 In vitro-Transkription/Translation und Myristoylierung der LeCPK1
Verschiedene Proteine in Hefe- und Säugetierzellen werden am N-Terminus co-translationell
über eine Peptidbindung mit Myristinsäure verkettet. Dabei katalysiert das Enzym NMyristoyltransferase die kovalente Bindung einer Myristinsäure an ein N-terminales Glycin,
das sich unmittelbar hinter dem Start-Methionin (das während der Translation abgespalten
wird) an erster Stelle des Polypeptides befindet (Russell et al., 1994).
Diese Protein-Acylierung scheint für viele Protein-Protein-Interaktionen und auch für die Protein-Membran-Assoziation bestimmter Proteine von entscheidender Bedeutung zu sein (Johnson et al., 1994). So schafft die ans Protein gebundene, gesättigte C14-Fettsäure eine erhöhte
Hydrophobizität, welche zusammen mit weiteren posttranslationellen Modifikationen ausreichend gross ist, um das Protein in der Plasmamembran verankern zu können (Yalovsky et al.,
1999).
Die Substratspezifität der N-Myristoyltransferase in Hefe- und Säugetierzellen ist aufgeklärt
worden (Towler et al., 1987; Towler et al., 1988): Das erwähnte Glycin ist für eine N-terminale
Myristoylierung absolut notwendig, ebenso unentbehrlich ist eine auf das Glycin folgende ungeladene Aminoäure. Ferner werden die Aminosäuren Serin und Threonin an Position 5 des
Polypeptides bevorzugt, aber nicht zwingend vorausgesetzt.
Obwohl die Protein-Myristoylierung in Pflanzen noch wenig untersucht ist, lässt die Aminosäuresequenz der LeCPK1 vermuten, dass auch dieses Enzym myristoyliert und eventuell in der
Plasmamembran verankert werden könnte. Um eine solche Verankerung nachzuweisen, wurde
der für die N-Myristoylierung essentielle Glycin-Rest mittels zielgerichteter Mutagenese gegen
Alanin ausgetauscht (Abb. 13) und eine mögliche Myristoylierung der Wildtyp-LeCPK1
(CDPKwt) und der Gly2Ala-Mutante (CDPKmut) in einem in vitro-Transkriptions-/Translationsexperiment untersucht.
Dazu wurden die beiden cDNAs in die XbaI-Schnittstelle des Vektors pBluescript SK(-) (im
folgenden Text pSK genannt) ligiert. Klone, die das cDNA-Insert in richtiger Orientierung relativ zum T7-Promotor des Vektors enthielten, wurden durch Restriktionsanalyse identifiziert
(hier nicht gezeigt) und die Identität der Klone wurde durch Sequenzanalyse bestätigt (Abb.
14).
3. Resultate
Seite 49
CDPKwt:
NH2–
Met – Gly – Gly – Cys – Phe – Ser – ...
CDPKmut:
NH2–
Met – Ala – Gly – Cys – Phe – Ser – ...
Abb. 13: N-terminale Aminosäuresequenzen der Wildtyp-LeCPK1 (CDPKwt) und der Gly2Ala-Mutante
CDPKmut. Bei der CDPKmut ist der für die N-Myristoylierung essentielle Glycin-Rest mittels zielgerichteter
Mutagenese gegen Alanin ausgetauscht worden.
PK33
+--------------->
T7
<----------------+
PK52
<-----------------+
PK54
<-----------------+
PK53
<-----------------+
T3
+------------------>
CONSENSUS+--------------------------------------------------------->
|------|------|------|------|------|------|------|------|------|0
200
400
600
800
1000
1200
1400
1600
1800
LePK52
+----->
PK53
+----------------->
T3
<------------------+
PK54
+------------------->
PK52
+--------------->
PKNT1
+---------------->
T7
+-------------->
PK33
<----------------+
CONSENSUS+----------------------------------------------->
|------|------|------|------|------|------|------|------|------|0
300
600
900
1200
1500
1800
2100
2400
2700
Abb. 14: Sequenzbestätigung der Konstrukte pSK-CDPKwt (oben) und pSK-CDPKmut (unten).
Für die Sequenzierung der CDPKwt- bzw. CDPKmut-cDNA wurden mehrere Primer für Teilbereiche (je ca. 400
Nukleotide) der LeCPK1-cDNAs verwendet. Zusätzlich wurden zwei Primer eingesetzt, die komplementär zu den
T7- und T3-Promotorsequenzen des Vektors pBluescript SK(-) waren. Durch Überlappung der Fragmente konnten
die gesamten cDNA-Sequenzen bestimmt und überprüft werden.
Diese Primerkarten wurden erstellt mit dem Programm GELASSEMBLE aus dem Softwarepaket GCG der University of Wisconsin Genetics Computer Group.
3. Resultate
Seite 50
Die Konstrukte wurden mit dem Restriktionsenzym NotI linearisiert. Anschliessend wurden die
cDNA-codierten Proteine in einem gekoppelten Weizenkeimextrakt in vitro-Transkriptions/Translationssystem in Anwesenheit von radioaktiv markierter [9,10-3H]-Myristinsäure oder
[35S]-Methionin exprimiert. Die Translationsprodukte wurden elektrophoretisch aufgetrennt
und die Inkorporation radioaktiven Methionins oder tritiierter Myristinsäure wurde fluorographisch nachgewiesen (Abb. 15).
Die Proteine CDPKwt und CDPKmut wurden in vergleichbaren Mengen translatiert (Abb. 15,
Spuren 3 und 4). Eine Markierung durch [9,10-3H]-Myristinsäure liess sich für die CDPKwt
(Abb. 15, Spuren 5 und 7), nicht aber für die CDPKmut (Abb. 15, Spuren 6 und 8) nachweisen.
Die LeCPK1 wird also in vitro tatsächlich myristoyliert, und diese Myristoylierung ist abhängig
von der intakten Erkennungssequenz.
3. Resultate
Seite 51
1
2
3
4
5
6
7
8
LuciferasecDNA
ohne
cDNA
pSKCDPKwt
pSKCDPKmut
pSKCDPKwt
pSKCDPKmut
pSKCDPKwt
pSKCDPKmut
97.4 kDa
66.2 kDa
Luciferase
LeCPK1
45.0 kDa
31.0 kDa
Einbau von [35S]-Met
Einbau von [9,10-3H]-Myristinsäure
Abb. 15: Myristoylierung der LeCPK1 in vitro.
Die cDNAs CDPKwt und CDPKmut wurden in vitro transkribiert und translatiert in Gegenwart von
[35S]-Met (Spuren 1-4) oder [9,10-3H]-Myristinsäure (Spuren 5-8).
Gezeigt ist eine Fluorographie nach elektrophoretischer Auftrennung der Translationsprodukte.
Spur 1:
Als Templat für die Translation wurde eine Luciferase-cDNA benutzt (Positivkontrolle).
Spur 2:
Transkription/Translation ohne cDNA-Templat (Negativkontrolle).
Spuren 3-4: Transkription/Translation der cDNAs pSK-CDPKwt und pSK-CDPKmut in Gegenwart
von [35S]-Met.
Spuren 5-8: Transkription/Translation der cDNAs pSK-CDPKwt und pSK-CDPKmut in Gegenwart von
[9,10-3H]-Myristinsäure. Es wurden 5 µl (Spuren 5 und 6) bzw. 10 µl (Spuren 7 und 8)
des in vitro-Translationsansatzes analysiert.
3. Resultate
Seite 52
3.7 Transiente Expression der Fusionsproteine CDPKwt-EGFP und
CDPKmut-EGFP in Zwiebelepidermiszellen
Nachdem im Abschnitt 3.6 gezeigt worden ist, dass die CDPKwt, nicht aber in die CDPKmut
N-terminal myristoyliert wird, wurden hier die Auswirkungen der Myristoylierung auf die Lokalisation der LeCPK1 in vivo untersucht.
Dazu wurden die beiden cDNAs, die für die CDPKwt und die CDPKmut codieren, in die XbaISchnittstelle des Vektors pcl60 ligiert. Klone, die das cDNA-Insert in richtiger Orientierung
relativ zum 35S-Promotor des Vektors enthielten, wurden durch Restriktionsanalyse identifiziert (hier nicht gezeigt), und die Identität der Klone wurde durch Sequenzierung bestätigt
(Abb. 16).
PK33
+--------------->
PKNT
<-----------------+
PK52
<--------------+
PK54
<------------------+
PK53
<---------------------+
CONSENSUS+--------------------------------------------------------->
|------|------|------|------|------|------|------|------|------|0
200
400
600
800
1000
1200
1400
1600
1800
LePK52
+-->
PK53
+------------------->
PK54
+----------------->
PK52
+----------------->
PKNT1
+----------------->
PK33
<--------------+
CONSENSUS+--------------------------------------------------------->
|------|------|------|------|------|------|------|------|------|0
200
400
600
800
1000
1200
1400
1600
1800
Abb. 16: Sequenzbestätigung der Konstrukte pcl60-CDPKwt (oben) und pcl60-CDPKmut (unten).
Für die Sequenzierung der CDPKwt- bzw. CDPKmut-cDNA wurden mehrere Primer für Teilbereiche (je ca. 450
Nukleotide) der LeCPK1-cDNAs verwendet. Zusätzlich wurden zwei Primer so eingesetzt, dass auch die angrenzenden Teile des Vektors, die das Insert umgeben, sequenziert wurden. Durch Überlappung der Fragmente konnten die gesamten cDNA-Sequenzen bestimmt und überprüft werden.
Diese Primerkarten wurden erstellt mit dem Programm GELASSEMBLE aus dem Softwarepaket GCG der University of Wisconsin Genetics Computer Group.
3. Resultate
Seite 53
Das Green Fluorescent Protein (GFP) ist ein fluoreszierendes Protein aus der pazifischen
Qualle Aequorea victoria (Chalfie und Tu, 1994) das bei Anregung mit Blaulicht (488 nm)
ohne die Zugabe von exogenen Substraten oder Kofaktoren Grünlicht (508 nm) emittiert. Proteine, die an das 26 kDa grosse GFP gekoppelt werden, können in vivo am Fluoreszenzmikroskop lokalisiert werden. Das hier eingesetzte EGFP (Enhanced GFP, Clontech) weist
nach Substitution zweier Aminosäuren des Chromophors eine gegenüber dem Wildtyp-GFP um
ein Mehrfaches erhöhte Fluoreszenz auf (Cubitt et al., 1995).
Mittels der Mikroprojektiltechnik wurden Zwiebelepidermiszellen mit den cDNA-Konstrukten
pcl60, pcl60-CDPKwt und pcl60-CDPKmut transformiert. Alle drei Plasmide enthielten die
cDNA für das EGFP unter der Kontrolle des 35S-Promotors. Die Konstrukte pcl60-CDPKwt
und pcl60-CDPKmut codierten dabei für die CDPKs in C-terminaler Fusion mit EGFP. Zur
transienten Expression der cDNAs wurden die Zellen nach der Transformation während mind.
24 h inkubiert und dann mittels eines spektralen, konfokalen Laser-Scanning Mikroskopes untersucht.
Das EGFP selbst (Abb. 17) liess sich sowohl im Cytoplasma als auch im Nukleus nachweisen,
wobei die Fluoreszenz im Vergleich mit den anderen Konstrukten relativ stark war. Die Vakuole, die bei den vollturgeszenten Epidermiszellen fast das ganze Zellvolumen erfüllt, blieb
ausgespart. Das Fusionsprotein CDPKwt-EGFP war im Bereich der Plasmamembran lokalisiert
(Abb. 18). Weder im Kern, noch im Cytoplasma war eine Fluoreszenz festzustellen. Das Fusionsprotein CDPKmut-EGFP befand sich hingegen (wie das EGFP selbst) im Cytoplasma und
im Zellkern, nicht aber im Bereich der Plasmamembran (Abb. 19). Offenbar ist für eine Assoziation mit der Plasmamembran eine intakte Myristoylierungsstelle erforderlich.
3. Resultate
Seite 54
V
N
50 µm
Abb. 17: Zwiebelepidermiszelle, transformiert mit pcl60.
Das transient exprimierte EGFP befindet sich im Cytoplasma und im Nukleus (N), nicht aber in der Vakuole (V).
(200-fache Vergrösserung, Überlagerung des Durchlichtbildes mit dem grünen Fluoreszenz-Signal)
PM
V
N
50 µm
Abb. 18: Zwiebelepidermiszelle, transformiert mit pcl60-CDPKwt.
Das transient exprimierte Fusionsprotein CDPKwt-EGFP befindet sich im Bereich der Plasmamembran (PM).
(200-fache Vergrösserung, Überlagerung des Durchlichtbildes mit dem grünen Fluoreszenz-Signal)
C
V
N
50 µm
Abb. 19: Zwiebelepidermiszelle, transformiert mit pcl60-CDPKmut.
Das transient exprimierte Fusionsprotein CDPKmut-EGFP befindet sich im Cytoplasma (C) und im Nukleus (N).
(200-fache Vergrösserung, Überlagerung des Durchlichtbildes mit dem grünen Fluoreszenz-Signal)
3. Resultate
Seite 55
3.8 Transiente Expression der Fusionsproteine CDPKwt-EGFP und
CDPKmut-EGFP in Lycopersicon peruvianum-Zellen aus Suspensionskultur
Im vorausgehenden Experiment wurde die mit dem EGFP fusionierte LeCPK1 heterolog in
Zwiebelepidermiszellen exprimiert. Dabei konnte die Wildtyp-Kinase im Bereich der Plasmamembran lokalisiert werden. Weil es sich bei der hier klonierten und untersuchten LeCPK1 um
ein Protein aus L. esculentum handelt und eine Rolle dieser Proteinkinase in der Alkalisierungsantwort von L. peruvianum-Zellen auf Systemin vermutet wird, wurden im vorliegenden
Experiment L. peruvianum-Zellen transformiert. Sieben Tage alte Zellen einer Suspensionskultur von L. peruvianum wurden also in ähnlicher Weise wie die Zwiebelepidermiszellen
mittels der Mikroprojektiltechnik mit den Konstrukten pcl60, pcl60-CDPKwt und pcl60CDPKmut transformiert. Anschliessend wurde die Lokalisation der transient exprimierten und
fluoreszierenden Proteine im spektralen, konfokalen Laser-Scanning Mikroskop untersucht.
Die L. peruvianum-Zellen, deren Durchmesser etwa achtmal kleiner war als die Länge der
Zwiebelepidermiszellen, wiesen eine für Suspensionskulturzellen typische kugelige Form auf.
Die Zentralvakuole wurde jeweils von vielen cytoplasmatischen Bereichen ("CytoplasmaSträngen") durchzogen. Weil die Zellen leicht plasmolysiert waren, hatte sich der Protoplast an
einigen Stellen von der Zellwand gelöst (Abb. 20 und 22).
Die Lokalisation der überexprimierten Proteine stimmte mit der in den Zwiebelepidermiszellen
weitgehend überein: Das EGFP selbst wurde sowohl im Cytoplasma als auch im Kern löslich
exprimiert, nicht aber in der Vakuole (Abb. 20). Das Fusionsprotein CDPKwt-EGFP war ausschliesslich im Bereich der Plasmamembran lokalisiert (Abb. 21). Das CDPKmut-EGFPFusionsprotein hingegen befand sich wie das EGFP selbst im Cytoplasma und im Kern (Abb.
22). Auch in den L. peruvianum-Zellen wirkte sich also das Fehlen einer Myristoylierungsstelle
in der CDPKmut auf die intrazelluläre Lokalisierung der Kinase aus.
3. Resultate
Seite 56
Abb. 20: Lycopersicon peruvianum-Zelle aus Flüssigkultur,
transformiert mit dem Konstrukt pcl60.
Das transient exprimierte EGFP befindet sich im Cytoplasma
(C) und im Nukleus (N), nicht aber in der Vakuole (V). Der
Protoplast hat sich an gewissen Stellen von der Zellwand
gelöst, was auf eine leichte Plasmolyse hindeutet.
V
N
(1000-fache Vergrösserung, Überlagerung des Durchlichtbildes mit dem grünen Fluoreszenz-Signal)
C
10 µm
PM
Abb. 21: Lycopersicon peruvianum-Zelle aus Flüssigkultur,
transformiert mit dem Konstrukt pcl60-CDPKwt.
V
Das transient exprimierte Fusionsprotein CDPKwt-EGFP
befindet sich im Bereich der Plasmamembran (PM). Im
Zellkern und den cytoplasmatischen Bereichen ist keine
Fluoreszenz sichtbar.
N
(1000-fache Vergrösserung, Überlagerung des Durchlichtbildes mit dem grünen Fluoreszenz-Signal)
10 µm
Abb. 22: Lycopersicon peruvianum-Zelle aus Flüssigkultur,
transformiert mit dem Konstrukt pcl60-CDPKmut.
C
Das transient exprimierte Fusionsprotein CDPKmut-EGFP
befindet sich im Cytoplasma und im Nukleus.
(1000-fache Vergrösserung, Überlagerung des Durchlichtbildes mit dem grünen Fluoreszenz-Signal)
V
N
10 µm
3. Resultate
Seite 57
3.9 Titration einer GST-CDPK-Lösung mit CaCl2 unter paralleler Aufnahme
des Fluoreszenzspektrums
Die CDPKs verfügen über eine C-terminale, Calmodulin-ähnliche Domäne mit bis zu vier
Ca2+-Bindestellen, sogenannten EF-Hand-Motiven. Es wird vermutet, dass durch Bindung von
freien Ca2+-Ionen die Calmodulin-ähnliche Domäne eine unmittelbar benachbarte Region der
katalytischen Domäne binden kann, wodurch das Enzym aktiviert wird (Binder et al., 1994;
Harmon et al., 1994; Yoo und Harmon, 1996). Die dadurch verursachte Konformationsänderung führt möglicherweise zu einer veränderten Tryptophan-Fluoreszenz. Hier sollte durch
Messung solcher Änderungen während der Titration der GST-CDPK mit CaCl2 die Dissoziationskonstanten für Calcium ermittelt werden.
Mit zunehmender Ca2+-Konzentration im Ansatz nahm die relative Fluoreszenz gegenüber den
Anfangswerten über das gesamte Spektrum nichtlinear ab (Abb. 23a), was auf eine Konformationsänderung der GST-CDPK nach Ca2+-Bindung hinweist. Nach der Titration wurde die steigende Ca2+-Konzentration im Ansatz gegen die bei 325 nm maximale, relative Fluoreszenzabnahme aufgetragen (Abb. 23b). Anschliessend wurde durch mathematische Interpolation versucht, die Messpunkte dem Graphen einer stöchiometrischen Funktion zuzuordnen.
Dabei beschrieb die zweifach hyperbolische Funktion
y = f(x) =
a∗x c∗x
+
b+ x d + x
x = Ca2+-Konzentration im Ansatz [µM]
y = Relative Fluoreszenzabnahme bei 325 nm [%]
den Verlauf der gegebenen Messpunkte am besten (mit einem Determinationskoeffizienten
Rsqr von 0.993), wenn die Konstanten b und d auf Werte von von 0.59 µM und 54.85 µM gesetzt wurden. b und d repräsentieren dabei zwei verschiedene Dissoziationskonstanten, die als
Mittelwerte aus zwei unabhängig durchgeführten Experimenten erhalten wurden.
Offenbar besitzen von den vier Ca2+-Bindestellen der LeCPK1 je zwei eine niedrige Dissoziationskonstante von 0.6 µM (bzw. eine hohe Ca2+-Affinität), während die anderen beiden Bindestellen eine hohe Dissoziationskonstante von 55 µM (bzw. eine niedrige Affinität für Ca2+)
aufweisen.
3. Resultate
Seite 58
Relative Fluoreszenz [%]
140
120
ohne Ca2+
100
80
0.46 mM Ca2+
60
40
20
A
0
300
320
340
360
380
400
Wellenlänge der Fluoreszenz [nm]
Relative Fluoreszenzabnahme [%]
bei 325 nm
50
40
30
20
Data fitting according to equation
f = a*x/(b+x)+c*x/(d+x)
10
b = Kd 1: 0.6 µM
d = Kd 2: 66 µM
0
B
0
100
200
300
400
500
Ca2+-Konzentration [µM]
Abb. 23: Relative Fluoreszenzabnahme der GST-CDPK bei der Titration mit CaCl2.
A: Bei der Titration einer 0.5 µM GST-CDPK-Lösung mit CaCl2 nimmt die relative Fluoreszenz nach Anregung
bei 280 nm über das gesamte Spektrum ab.
B: Auftragung der relativen Fluoreszenzabnahme bei 325 nm. Die Punkte repräsentieren die gemessenen Werte,
während die ausgezogene Linie den Graphen der angegebenen, interpolierten Funktion darstellt. Die angegebenen Konstanten b und d der Funktion entsprechen zwei verschiedenen Dissoziationskonstanten der vier
Ca2+-Bindestellen der GST-CDPK.
Die GST-CDPK-Lösung lag in 50 mM HEPES-Puffer pH 7.5 vor. Die CaCl2-Titration erfolgte in 2 µl-Schritten
bis zu einer Konzentration von 0.46 mM im Ansatz. Gezeigt ist der erste von zwei unabhängig durchgeführten
Versuchen. Die Daten wurden mit den Programmen Excel 97 (Microsoft) und SigmaPlot 6.0 (SPSS Inc.) ausgewertet.
4. Diskussion
Seite 59
IV. DISKUSSION
Bei einer ersten Charakterisierung der LeCPK1 nach der Klonierung des Enzyms aus einer
cDNA-Bibliothek von Lycopersicon esculentum wurde festgestellt, dass eine FusicoccinBehandlung von Tomatenblättern zu einer erhöhten Akkumulation von LeCPK1-Transkripten
führte (Stalder, 2000).
Es wurde deshalb vorgeschlagen, dass die LeCPK1 an der Regulation von Abwehrreaktionen
der Tomatenpflanze bei pathogener Infektion oder Verwundung durch Herbivoren beteiligt sein
könnte. Eine mögliche Funktion der LeCPK1 wäre dabei die Modulierung der Aktivität der
Plasmamembran-H+-ATPase, welche an den erwähnten Abwehrreaktionen beteiligt ist (Blum
et al., 1988; Johansson et al., 1993;Vera-Estrella et al., 1994; Schaller und Oecking, 1999).
Um eine Rolle in einer Pathogen-induzierten Signaltransduktionkette einnehmen zu können,
müsste die LeCPK1 durch Ca2+-Konzentrationen, wie sie in der lebenden Zelle auftreten, aktiviert werden können. Zudem müsste sie Zugang zum potentiellen Substrat besitzen, was bei
einer Co-Lokalisation der LeCPK1 und der H+-ATPase an der Plasmamembran gewährleistet
wäre. Ausserdem wäre es notwendig, dass die LeCPK1 die H+-ATPase als Substrat erkennen
und phosphorylieren könnte.
Diese drei Bedingungen für eine Funktion der LeCPK1 in einer Pathogen-induzierten Signaltransduktionskette wurden im Rahmen der vorliegenden Arbeit untersucht und sollen im Folgenden diskutiert werden.
4. Diskussion
Seite 60
4.1 Die Bindung von Calcium an die LeCPK1
Es wurde bereits von Stalder gezeigt, dass die C-terminale Domäne der LeCPK1 eine funktionelle, Ca2+-bindende Domäne ist (Stalder, 2000). Für die mit GST fusionierte LeCPK1, nicht
aber ein um 143 Aminosäuren am C-Terminus verkürztes Fusionsprotein, konnte die Bindung
von
45
Ca2+ nachgewiesen werden. Zudem wurde gezeigt, dass die Ser/Thr-Proteinkinase-
Aktivität der LeCPK1 sowohl von Ca2+ als auch von der Ca2+-bindenden Domäne abhängig ist
(Stalder, 2000). Diese Befunde stehen im Einklang mit gängigen Vorstellungen, nach denen es
in Folge von Ca2+-Bindung zu einer Konformationsänderung pflanzlicher CDPKs kommt, die
zur Aktivierung der Kinase führt. Im inaktiven Zustand blockiert die zentrale, autoregulatorische Domäne als Pseudosubstrat den Zugang zum aktiven Zentrum. Eine Ca2+-induzierte Konformationsänderung entfernt die autoregulatorische Domäne, wodurch das aktive Zentrum zugänglich und die Proteinkinase aktiviert wird (Harmon et al., 1994; Yoo und Harmon, 1996;
Huang et al., 1996).
Derartige Konformationsänderungen gehen oft mit Veränderungen im Fluoreszenzspektrum
des Proteins einher, die auf Veränderungen in der molekularen Umgebung aromatischer Aminosäuren (insbesondere Trp) zurückzuführen sind. In der Tat finden sich in der katalytischen
Domäne der LeCPK1 vier Trp-Reste (an den Positionen 289, 306, 329 und 362; Abb. 4 auf
Seite 11). Infolge veränderter Exposition dieser Trp-Reste nach Ca2+-Bindung und dadurch
induzierter Konformationsänderung ist bei der Aktivieung der LeCPK1 eine Änderung der
Tryptophan-Fluoreszenz zu erwarten.
Bei Titration der Proteinkinase mit CaCl2 wurde mit zunehmender Menge gebundenen Calciums eine Abnahme der relativen Fluoreszenz über das gesamte Spektrum festgestellt, welche
bei 325 nm am ausgeprägtesten war. Dabei wurden zwei Klassen von Calcium-Bindestellen
beobachtet, die sich deutlich in ihrer Affinität unterschieden. Die grösste Fluoreszenzänderung
war bei Absättigung der hochaffinen Bindestellen (Kd = 0.6 µM) zu beobachten, bei der Konzentration also, die vermutlich in vivo zur Aktivierung des Enzyms führt. Bei Sättigung der
weniger affinen Bindestellen (Kd = 55 µM) waren dagegen nur noch geringfügige Änderungen
festzustellen. Allerdings muss hier einschränkend gesagt werden, dass die Bindung von Calcium in Abwesenheit von Substraten gemessen wurde. Es ist durchaus möglich, dass sich die
Affinität für Ca2+ in Anwesenheit eines Kinasesubstrats von den gemessenen Werten unterscheidet (Lee et al., 1998).
4. Diskussion
Seite 61
Die Ca2+-bindende Domäne pflanzlicher CDPKs weist strukturelle Verwandtschaft mit Calmodulin auf. Calmodulin ist ein in eukaryotischen Zellen ubiquitär vorhandenes, regulatorisches
Protein mit einem Molekulargewicht von 17 kDa, das durch die Bindung von Ca2+-Ionen an
vier Bindestellen einer Konformationsänderung unterworfen ist (Alberts et al., 1994). Bei dieser Veränderung der räumlichen Struktur werden zwei hydrophobe Taschen exponiert, mit denen Calmodulin an viele verschiedene Zielproteine binden und diese in ihrer Aktiviät modulieren kann. Die Ca2+-Bindestellen von Calmodulin werden durch vier Helix-Loop-Helix-Motive,
sogenannte EF-Hand-Domänen, gebildet. Eine solche Bindestelle besteht aus 36 Aminosäuren,
von denen zwölf an der Koordination des Ca2+-Kations ins Protein beteiligt sind, während die
übrigen Reste zwei a-Helices bilden, welche die Bindestelle umgeben (Abb. 24b). Je zwei benachbarte EF-Hand-Motive werden durch ein antiparalleles ß-Faltblatt verbunden, das durch
eine Konformationsänderung eine kooperative Bindung von Ca2+ an die beiden Bindestellen
ermöglicht. Eine 2 nm lange, flexible a-Helix schliesslich verbindet das EF-Hand-Paar am NTerminus des Calmodulins mit den zwei Bindestellen am C-Terminus (Abb. 24a, Babu et al.,
1985).
Die Ca2+-Bindung von Calmodulin wurde eingehend untersucht, u.a. mittels isothermaler Mikro-Titrationskalorimetrie (Gilli et al., 1998). Dabei stellte sich heraus, dass die zwei C-terminalen Bindestellen mit den Dissoziationskonstanten von 0.54 µM und 0.81 µM hochaffin
sind, während die gegenüberliegenden EF-Hand-Motive niedrigaffine Bindestellen enthalten
(Kd = 2.27 µM und 10 µM). Diese Asymmetrie setzt sich auch in der Art der Ligandenbindung
fort. So sind die Bindungen auf der C-terminalen Seite Enthalpie- und Entropie-getrieben, während die diejenige am N-Terminus ausschliesslich Entropie-getrieben ist.
4. Diskussion
Seite 62
Abb. 24: Calmodulin aus dem Hirngewebe von Homo sapiens.
A Dreidimensionales Strukturmodell von Calmodulin. Jeweils ein Ca2+-Ion wird in einem Helix-Loop-HelixMotiv, der sogenannten EF-Hand-Domäne, gebunden. Je zwei EF-Hand-Domänen werden durch ein ß-Faltblatt
zusammengehalten und mit den gegenüberliegenden zwei Bindestellen über eine lange, flexible a-Helix verbunden. (nach Babu et al., 1988; Strukturmodell von B. Rupp, Lawrence Livermore National Laboratory, University
of California)
B Schematische Aufzeichnung der Peptidsequenz von Calmodulin. Jeweils zwölf Aminosäuren bilden einen
Loop und sind an der Ca2+-Bindung beteiligt. Dabei wird das Kation siebenfach koordiniert, wobei als siebter
Bindungspartner ein Wassermolekül (nicht gezeigt) dient. Die grünlich gefärbten Aminosäuren bilden a-Helices,
die ungefärbten ß-Faltblatt-Strukturen (nach Babu et al., 1988; Darstellung von J. I. Garcia, St. Edward's University, Austin, Texas).
Für die in dieser Arbeit charakterisierte LeCPK1 sagt das Programm "PROSITE" (http://www.expasy.ch) ebenfalls vier EF-Hand-Motive voraus (Abb. 4 auf Seite 11). Die wichtige Rolle
dieser EF-Hand-Domänen in der Ca2+-Bindung und Regulation von Ca2+-abhängigen Proteinkinasen ist von Hong et al. gezeigt worden (Hong et al., 1996).
Es ist wahrscheinlich, dass die bei der Titration der GST-CDPK beobachteten zwei Klassen
von Ca2+-Bindestellen den zwei hoch- und niederaffinen Bindestellen des Calmodulins entspre-
4. Diskussion
Seite 63
chen. Auch für eine CDPK aus Plasmodium falciparum ist durch zielgerichtete Mutagenese
gezeigt worden, dass sich die vier EF-Hand-Motive funktionell unterscheiden. Mutationen in
den zwei Bindestellen nahe der katalytischen Domäne hatten drastische Effekte auf die Ca2+Bindung und die Aktivität der Kinase, während Mutationen in den zwei C-terminalen EFHand-Motiven nur geringfügige Konsequenzen hatten (Zhao et al., 1994). Dieser Befund unterstützt die Interpretation, dass Ca2+-Bindung an die hochaffine Klasse von Bindestellen relevant
für die Aktivierung der LeCPK1 ist. In der Tat scheint die Bindung von 1 bis 2 MolÄquivalenten Ca2+ ausreichend für die Aktivierung der CDPKs zu sein (Zhao et al., 1994; Lee
et al., 1998). Die cytoplasmatische Konzentration freien Calciums liegt im Ruhezustand typischerweise bei 0.1 µM oder tiefer und erhöht sich bei Stimulation der Zelle auf Werte um 1
µM. Mit einer Dissoziationskonstante von 0.6 µM für die hochaffinen Bindestellen ist die
LeCPK1 in der Lage, mit einer Aktivierung auf diese Änderung der Konzentration freien Calciums zu reagieren.
In weitergehenden Versuchen könnten mittels isothermaler Titrations-Mikrokalorimetrie alle
vier Dissoziationskonstanten sowie die thermodynamischen Parameter Bindungsenthalpie ∆H,
freie Reaktionsenthalpie ∆G sowie die Entropie ∆S der Ca2+-Bindung an die LeCPK1 bestimmt
werden. Erst die Aufklärung der dreidimensionalen Struktur einer CDPK jedoch wird die Konformationsänderung der Kinase bei Ca2+-Bindung endgültig bestätigen können.
Abschliessend soll darauf hingewiesen werden, dass sowohl für die Bestimmung der Ca2+Affinität als auch in den H+-ATPase-Phosphorylierungs-Experimenten ein GST-Fusionsprotein
der LeCPK1 eingesetzt worden ist. Obwohl die Glutathion-S-Transferase lediglich ein Viertel
des Fusionsproteines GST-CDPK ausmacht und das Fusionsprotein alle Charakteristika einer
CDPK aufwies, ist nicht ganz auszuschliessen, dass es aufgrund dieser Modifikation im Vergleich zur Wildtyp-Kinase veränderte Eigenschaften besitzt. Alle Versuche, den GST-Teil des
Fusionsproteines nach erfolgter Reinigung mit dem Faktor Xa proteolytisch abzuspalten,
scheiterten jedoch, da diese Protease die Peptidsequenz nicht nur an der dafür vorgesehenen
Schnittstelle, sondern auch innerhalb der LeCPK1-Sequenz schnitt (nicht gezeigt). Der Ort der
internen Spaltung wurde durch N-Terminale Sequenzierung des Abbauproduktes ermittelt
(nicht gezeigt). Aber auch durch Zerstörung dieser Erkennungssequenz innerhalb der LeCPK1Sequenz durch zielgerichtete Mutation zweier Aminosäuren konnte die unerwünschte Proteolyse durch den Faktor Xa nicht ganz verhindert werden (Frick, 2001).
4. Diskussion
Seite 64
4.2 Subzelluläre Lokalisation der LeCPK1
Die vorgeschlagene Rolle der LeCPK1 als Regulator der Plasmamembran-H+-ATPase erfordert
eine räumliche und zeitliche Co-Lokalisation von H+-ATPase und LeCPK1. Stalder zeigte bereits, dass die LeCPK1 in Blättern von Tomatenpflanzen exprimiert wird und dass die Transkripte nach Behandlung mit Fusicoccin akkumulieren (Stalder, 2000). Die subzelluläre Lokalisation der LeCPK1 ist aber bisher nicht untersucht worden. Die Primärstruktur der LeCPK1
weist keine ausgedehnten Bereiche hydrophober Aminosäuren auf, die auf Membranständigkeit
hindeuten würden. Eine solche könnte daher allenfalls durch posttranslationelle Modifikationen
bewirkt werden. So wäre eine Lipid-Modifizierung durch kovalente Bindung von mehrfach
gesättigten Fettsäuren (Myristinsäure, C14 oder Palmitinsäure, C16) oder Prenylierung (Farnesylierung, C15 oder Geranylgeranylierung, C20) denkbar (Resh, 1999 und Rodriguez-Conception et al., 1999). Eine Myristoylierung des Aminoterminus ist nach co-translationeller Abspaltung des Start-Methionins möglich. Hierbei wird die Aminogruppe eines N-terminalen
Glycin-Restes mit der Carboxylatgruppe der Myristinsäure verknüpft. Befindet sich in der Nähe des Myristinsäure-bindenden Glycins ein Cystein-Rest, kann das Protein an dieser Stelle
palmitoyliert werden (Mumby, 1997). Dabei wird Palmitinsäure über eine reversible Thioesterbindung durch eine Palmitoyltransferase an die Sulfhydrylgruppe des Cysteins gebunden
(Casey, 1995).
Für eine Verankerung des Proteins in der Plasmamembran reicht alleinige Myristoylierung
nicht aus (Peitzsch und McLaughlin, 1993). Die "kinetic bilayer trapping"-Hypothese postuliert, dass ein myristoyliertes Protein zwar mit der Plasmamembran assoziieren kann, aber erst
durch eine dort stattfindende Palmitoylierung in der Membran verankert wird (Abb. 25a und
25c, Shahinian und Silvius, 1995). Eine Myristoylierung an Gly2 erleichtert die Palmitoylierung
an Cys3, ist aber dafür nicht unbedingt notwendig (Degtyarev et al., 1994).
Im Falle der Prenylierung kommt es zur Bildung einer Thioetherbindung zwischen Farnesyl
bzw. Geranylgeranyl und dem Cystein-Thiol einer konservierten, C-terminalen Sequenz, der
sogenannten CaaX-Box. In diesem Motiv repräsentiert a eine beliebige aliphatische Aminosäure und X im Falle von Geranylgeranylierung ein Leucin, im Falle von Farnesylierung ein Serin,
Methionin, Cystein, Alanin oder Glutamin (Zhang und Casey, 1996; Rodriguez-Conception et
al., 1999). Bei der Prenylierung werden alle C-terminal vom modifizierten Cystein liegenden
Aminosäuren abgespalten und das neue Carboxy-Ende methyliert. Wie bei der Myristoylierung
4. Diskussion
Seite 65
und Palmitoylierung kann auch durch Prenylierung die subzelluläre Lokalisation eines Proteins
beeinflusst werden. Ausserdem werden durch die hydrophoben Prenyl-Gruppen unter Umständen neue Protein-Protein-Interaktionen möglich (Rodriguez-Conception et al., 1999).
Neben den erwähnten kovalenten Modifikationen spielt auch die Nettoladung des Proteins für
eine mögliche Membran-Assoziation eine Rolle; ist sie positiv, oder besitzt das Protein eine
exponierte, polybasische Domäne, so ist eine Interaktion mit den negativ geladenen, polaren
Kopfgruppen der Membran-Phospholipide auch dann möglich, wenn das Protein nur einfach
acyliert vorliegt (Abb. 25b, Bhatnagar und Gordeon, 1997). Gleichmassen ist eine Verankerung
eines einfach acylierten Proteins möglich, wenn dieses mit einem anderen Membranprotein
interagiert und die Assoziation mit der Plasmamembran dadurch unterstützt wird (Abb. 25d).
Durch eine solche Interaktion kann ein acyliertes Protein auch spezifisch mit der Membran
eines bestimmten Organells interagieren, an der sich der Bindungspartner befindet.
A
B
Myristinsäure und
polybasische
Domäne
C
Myristinsäure und Palmitinsäure
D
Myristinsäure
und Protein-ProteinInteraktion
Myristinsäure
Abb. 25: Die Membran-Assoziation von myristoylierten Proteinen (nach Resh, 1999)
A: Für die Verankerung eines einfach myristoylierten Proteines in der Membran sind weitere Faktoren erforderlich: siehe B-D.
B: Eine polybasische Domäne des Proteins ermöglicht zusätzliche, elektrostatische Wechselwirkungen mit den
sauren Kopfgruppen der Phospholipide.
C: Eine oder zwei zusätzliche Palmitinsäureketten erhöhen die hydrophoben Interaktionen mit der Membran.
D: Auch Protein-Protein-Interaktionen mit membrangebundenen Proteinen können die Membraninteraktion von
einfach acylierten Proteinen verstärken.
4. Diskussion
Seite 66
Während eine Prenylierung der LeCPK1 auszuschliessen ist, deutet die aminoterminale Sequenz des Enzyms auf eine mögliche Modifizierung durch Myristinsäure und Palmitinsäure
hin. Eine kovalente Bindung der Myristinsäure wurde experimentell nachgewiesen und erwies
sich als abhängig vom Glycin-Rest an zweiter Position des Polypeptids (siehe Abschnitt 3.6).
Ein Glycin-Rest an dieser Position wird als essentiell für die Myristoylierung erachtet (Johnson
et al., 1994). Übereinstimmend war im Falle der Gly2Ala-Mutante (CDPKmut) keine Myristoylierung nachzuweisen. Eine Palmitoylierung an Cys4 der LeCPK1 ist wahrscheinlich, wurde
aber im Rahmen dieser Arbeit nicht untersucht. Darüber hinaus weist der Aminoterminus der
LeCPK1 auch einige basische Aminosäuren auf (Lys7 und Lys8, Abb. 26), die eine MembranAssoziation der LeCPK1 zusätzlich unterstützen könnten.
Myristat
Palmitat
+
+
Gly – Gly – Cys – Phe – Ser – Lys – Lys – ...
Abb. 26: Hypothetische Struktur des N-Terminus der posttranslationell modifizierten LeCPK1.
Das Start-Methionin wurde bei der Translation abgespalten. Der Glycin-Rest wurde bei der CDPKmut durch ein
Alanin ersetzt, was mit hoher Wahrscheinlichkeit sowohl eine Myristoylierung als auch eine Palmitoylierung verunmöglichte.
Eine Aminoterminale Myristoylierung wurde in vitro auch für eine CDPK aus Zucchini nachgewiesen (Ellard-Ivey et al., 1999). Bei einer CDPK aus Oryza sativa konnte in vitro neben der
Myristoylierung auch eine Palmitoylierung der Proteinkinase gezeigt werden (Martin und
Busconi, 2000).
Die subzelluläre Lokalisation der LeCPK1 wurde nach transienter Expression in Fusion mit
dem Enhanced Green Fluorescent Protein (EGFP) untersucht. Die LeCPK1 befand sich ausschliesslich im Bereich der Plasmamembran, sowohl in transformierten Zellen der Zwiebelepidermis als auch in Zellen von Lycopersicon peruvianum aus Suspensionskultur (siehe Abschnitte 3.7 und 3.8). Im Gegensatz dazu erwies sich die Gly2Ala-Mutante der LeCPK1 als
löslich und fand sich im Cytoplasma und im Kern, ebenso wie das EGFP selbst. Eine Myristoylierung an Gly2 und die vermutlich sich anschliessende Palmitoylierung an Cys4 sind also
notwendig und hinreichend für die Lokalisierung der LeCPK1 auf der cytoplasmatischen Seite
der Plasmamembran.
4. Diskussion
Seite 67
Es ist bemerkenswert, dass das nicht-myristoylierte Fusionsprotein CDPKmut-EGFP im Kern
vorzufinden war, obwohl es mit einem Molekulargewicht von 87 kDa im Gegensatz zum EGFP
selbst (26 kDa) eigentlich zu gross ist, um passiv vom Cytoplasma durch die Kernporen in den
Nucleus zu diffundieren (Nigg, 1997; Buchanan et al., 2000).
Ein passiver Eintritt in den Kern mag durch die starke, transiente Überexpression des Proteins
im Cytoplasma begünstigt sein. Eine andere Erklärungsmöglichkeit wäre, dass die AminosäureSequenz von EGFP ein schwaches Kernlokalisierungssignal enthält, welches bei normaler Myristoylierung nicht zum Tragen kommt. In der Tat gleicht das Motiv Pro347-Arg348-Lys349Arg350 der LeCPK1 dem Kernlokalisierungssignal des "SV40 largeTAntigen" (gemäss Sequenzvergleich mit dem Programm "PSORT" auf http://www.expasy.ch).
Es wäre also denkbar, dass die LeCPK1 unter bestimmten Umständen auch im Kern auftritt.
Obwohl es sich nämlich bei den diskutierten Lipid-Modifikationen um kovalente Veränderungen des Proteins handelt, ist dadurch die Lokalisation des Proteins nicht notwendigerweise statisch und unveränderlich. So ist beispielsweise Recoverin, ein Ca2+-bindendes Protein, das die
Membran-assoziierte Rhodopsinkinase in den retinalen Stäbchenzellen von Vertebraten inhibiert, stets myristoyliert. Nur in Folge von Ca2+-Bindung aber wird die Myristinsäurekette so
exponiert, dass eine reversible Verkankerung in der Plasmamembran und eine Inaktivierung der
Rhodopsinkinase möglich ist. Ca2+ ist hier also Regulator für den Aufenthalts- und Wirkungsort des Recoverin-Proteines (Ames et al., 1997). Auch das in Flagellen von Trypanosoma cruzi
vorkommende "flagellar calcium binding protein", das N-terminal sowohl myristoyliert als
auch palmitoyliert wird, assoziiert nur nach Ca2+-Bindung mit der Plasmamembran des Flagellums (Godsel und Engman, 1999).
Ein ähnlicher Mechanismus könnte auch im Falle der LeCPK1 zu einer Stimulus-abhängigen
Lokalisation im Kern oder der Plasmamembran führen. Viele der bisher untersuchten CDPKs
sind im Kern (Li et al., 1991, Pisum sativum) und/oder in Assoziation mit der Plasmamembran
(Schaller et al., 1992, Avena sativa; Klimczak und Hind, 1990, Hordeum vulgare; Ivata et al.,
1998, Nicotiana tabacum; Abo-El-Saad und Wu, 1995, Oryza sativa; Verhey et al., 1993,
Cucurbita pepo; Baizabal-Aguirre und de la Vara, 1997, Beta vulgaris; Ohto und Nakamura,
1995, Nicotiana tabacum) nachgewiesen worden. Kürzlich wurde bei der Charakterisierung
einer CDPK aus Mesembryanthemum crystallinum festgestellt, dass die Proteinkinase abhängig
von der extrazellulären Ca2+-Konzentration entweder Plasmamembran-assoziiert oder löslich
im Kern lokalisiert vorliegt (Patharkar und Cushman, 2000). Ein derartiges Phänomen war al-
4. Diskussion
Seite 68
lerdings bei transienter Expression von CDPKwt-EGFP in Zellen von Lycopersicon peruvianum nicht zu beobachten. Auch nach Chelatierung extrazellulären Calciums durch EGTA oder
nach Behandlung der Zellsuspension mit Systemin erwies sich das Fusionsprotein als Plasmamembran-assoziiert. Die Signifikanz des putativen Kernlokalisierungssignals bleibt also vorerst
ungeklärt.
4.3 Phosphorylierung der Plasmamembran-H+-ATPase
In den Abschnitten 3.7 sowie 3.8 wurde gezeigt, dass die untersuchte LeCPK1 in vivo Plasmamembran-assoziiert ist. Weil sie sich damit in der Nähe der Plasmamembran befindet, wäre es
denkbar, dass die Protonenpumpe ein Substrat der Proteinkinase ist.
Die Aktivität der Plasmamembran-H+-ATPase wird u.a. durch die autoinhibitorisch wirkende
C-terminale Domäne moduliert. Werden die letzten 51 Aminosäuren des C-Terminus der H+ATPase AHA2 von Arabidopsis thaliana durch Trypsin-Behandlung entfernt, nimmt die protonenpumpende Aktivität der H+-ATPase zu (Palmgren et al., 1990 und Palmgren et al., 1991).
Bereits 1988 wurde gezeigt, dass die Plasmamembran-H+-ATPase aus Wurzeln von Avena sativa Ca2+-abhängig phosphoryliert wird (Schaller, 1988). Ferner wurde festgestellt, dass die H+ATPase aus Blättern von Spinacia oleracea an Thr948, der zweitletzten Aminosäure am CTerminus der Protonenpumpe, phosphoryliert wird (Olsson et al., 1998).
Es wäre also denkbar, dass die LeCPK1 die H+-ATPase im Bereich des C-Terminus phosphorylieren und damit die Aktivität der Protonenpumpe beeinflussen kann, was im Rahmen dieser
Arbeit untersucht wurde.
Im Phosphorylierungs-Experiment (siehe Abschnitt 3.2) wurde gezeigt, dass die LeCPK1 die
C-Termini GST-CT56 und GST-CT66 der Plasmamembran-H+-ATPase in vitro phosphorylieren kann. Durch Abspaltung des GST-Anteils konnte gezeigt werden, dass die Phosphorylierung am C-Terminus selbst und nicht etwa am GST-Anteil des Fusionsproteins stattfindet
(siehe Abschnitt 3.4). Dies steht mit ähnlichen Versuchen im Einklang, bei denen ebenfalls die
C-terminale Region einer Plasmamembran-H+-ATPase aus Wurzelzellen von Zea mays durch
eine (unbekannte) Ca2+-abhängige Proteinkinase in vitro phosphoryliert wurde (Camoni et al.,
1998).
4. Diskussion
Seite 69
Die Tatsache, dass praktisch keine Unterschiede zwischen der Phosphorylierung des längeren
(66 AS) und des kürzeren (56 AS) C-Terminus feststellbar waren, wurde bereits im Ergebnisteil diskutiert. Offenbar befinden sich an den zehn zusätzlichen Aminosäuren des längeren CTerminus keine Phosphorylierungsstellen. Dies ist insofern erstaunlich, als doch durch diese
zehn zusätzlichen Aminosäuren eine mögliche Erkennungsstelle für pflanzliche CDPKs generiert wird (...KLFS..., Abb. 27). Die von den CDPKs erkannte Konsensus-Sequenz lautet
R/KxxS/T (Roberts und Harmon, 1992).
Von den anderen Ser/Thr-Resten des CT56 befinden sich keine in einem Kontext, der dem obigen Konsensus von CDPK-Substraten entspricht. Im Falle von Thr923 und Ser930 (Abb. 27) befindet sich aber vier bzw. fünf Reste zuvor eine basische Aminosäure. Obwohl diese Distanz
nicht optimal ist (in der Konsensus-Sequenz befindet sich die basische Aminosäure drei Reste
vor dem Ser/Thr), mag sie zur Substraterkennung ausreichen.
Eine weitere Möglichkeit wäre die Phosphorylierung von Threonin947 (Abb. 27), wie dies kürzlich bei der (auch hier verwendeten) Plasmamembran-H+-ATPase PMA2 von Nicotiana plumbaginifolia (Svennelid et al., 1999; Maudoux et al., 2000) gezeigt worden ist. Diese Stelle kann
nach Phosphorylierung ein 14-3-3-Protein-Dimer binden und so die H+-ATPase aktivieren.
509
DQLAIGKETG RRLGMGTNMY PSSALLGQTK DESIASLPID ELIEKADGFA GVFPEHKYEI
569
VKRLQARKHI CGMTGDGVND APALKKADIG IAVDDATDAA RSASDIVLTE PGLSVIISAV
629
LTSRAIFQRM KNYTIYAVSI TIRIVLGFML LALIWKFDFP PFMVLIIAIL NDGTIMTISK
689
DRVKPSPLPD SWKLAEIFTT GVVLGGYLAM MTVIFFWAAY ETDFFPRVFG VSTLQKTATD
749
DFRKLASAIY LQVSTISQAL IFVTRSRSWS FVERPGLLLV VAFLIAQLVA TLIAVYANWA
809
FAAIEGIGWG WAGVIWLYNL VFYFPLDIIK FLIRYALSGR AWDLVLEQRI AFTRKKDFGK
869
EQRELQWAHA QRTLHGLQVP DTKLFSEATN FNELNQLAEE AKRRAEIARQ RELHTLKGHV
929
ESVVKLKGLD IETIQQSYTV-COOH
Abb. 27: Die 440 C-terminalen Aminosäuren der Plasmamembran-H+-ATPase PMA2 von Nicotiana
plumbaginifolia. Das vollständige Protein inkl. N-Terminus umfasst 948 Aminosäuren.
Rot:
Blau:
Kursiv:
Sequenz des verwendeten Teilpeptides CT66, das die 66 C-terminalen AS umfasst.
Sequenz des verwendeten Teilpeptides CT56, das die 56 C-terminalen AS umfasst.
Die zusätzlichen 10 Aminosäuren des Teilpeptides CT66.
Das Thr947, welches durch Phosphorylierung ein 14-3-3-Protein-Dimer binden kann.
Mögliche Erkennungsstellen für eine Phosphorylierung durch die GST-CDPK
(phosphoryliert würden Ser894, Thr923 und/oder Ser930).
4. Diskussion
Seite 70
Der Ort der Phosphorylierung soll im Rahmen weiterführender Arbeiten in Zusammenarbeit
mit M. Piotrowski (Ruhr-Universität, Bochum) mit Hilfe der Massenspektrometrie eindeutig
bestimmt werden.
Um mehr über die Auswirkungen der gezeigten Phosphorylierung und damit die Funktion der
LeCPK1 zu erfahren, wurde ein Experiment durchgeführt, bei dem Plasmamembran-Vesikel in
An- oder Abwesenheit der GST-CDPK inkubiert wurden und anschliessend die Aktivität der
Plasmamembran-H+-ATPase gemessen wurde.
In bisher durchgeführten Experimenten zeigte eine Phosphorylierung der H+-ATPase keine
einheitlichen Auswirkungen auf die Aktivität der Protonenpumpe. So führte eine Dephosphorylierung der H+-ATPase von Lycopersicon esculentum durch eine Phosphatase nach Zugabe eines Elicitors von Cladosporium fulvum zu einer Aktivierung der Protonenpumpe (Vera-Estrella
et al., 1994). Eine anschliessende Ca2+-abhängige Rephosphorylierung, die von zwei verschiedenen Proteinkinasen durchgeführt wurde, deaktivierte die Protonenpumpe wieder (Xing et al.,
1996). In ähnlicher Weise führte die Dephosphorylierung einer Plasmamembran- H+-ATPase
aus Nicotiana plumbaginifolia zu einer Aktivierung des Enzyms (Desbrosses et al.. 1998).
Auch Experimente mit rekonstituierten Proteoliposomen aus Beta vulgaris (Lino et al., 1998)
zeigten, dass die H+-ATPase-Aktivität durch Ca2+-abhängige Phosphorylierung reduziert wird.
In den erwähnten Beispielen führte die Phosphorylierung der H+-ATPase jeweils zu einer Deaktivierung der Protonenpumpe. Bei einer Phosphorylierung am C-Terminus des Enzyms
kommt es jedoch zu einer Aktivierung des Enzyms. So wird die Plasmamembran-H+-ATPase
aus Nicotiana plumbaginifolia durch eine unbekannte Proteinkinase an der zweitletzten, konservierten Aminosäure des C-Terminus (dem Thr947) phosphoryliert (Camoni et al., 1999;
Svennelid et al., 1999; Fuglsang et al., 1999). Dies ermöglicht die Bindung eines 14-3-3Protein-Dimers an den C-Terminus, wodurch die Protonenpumpe aktiviert wird (Oecking et al.,
1997; Jahn et al., 1997; Maudoux et al., 2000). Auch die H+-ATPase in Schliesszellen von Vicia faba wird bei Bestrahlung mit Blaulicht durch Phosphorylierung der zweitletzten Aminosäure am C-Terminus und anschliessende Bindung von 14-3-3-Proteinen aktiviert (Kinoshita
und Shimazaki, 1999).
4. Diskussion
Seite 71
Die unterschliedlichen Konsequenzen einer Phosphorylierung der Plasmamembran-H+-ATPase
werden mit dem in der Einführung erwähnten Regulationsmodell (Morsomme und Boutry,
1999; Abb. 3 auf Seite 8) wie folgt erklärt: Nach Phosphorylierung an einer bisher nicht ermittelten Stelle der H+-ATPase (evtl. ausserhalb des C-Terminus) befindet sich die Protonenpumpe
in einem inaktiven Zustand (Abb. 3b). Ist das Enzym hingegen wie oben beschrieben am konservierten Threonin des extremen C-Terminus phosphoryliert, erfolgt die Bindung eines 14-33-Protein-Dimers und die Aktivierung der H+-ATPase (Abb. 3c) . Eine gänzlich nicht-phosphorylierte H+-ATPase besitzt eine vergleichsweise niedrige Grundaktivität (Abb. 3a). Falls die
LeCPK1 den C-Terminus der H+-ATPase auch dann phosphoryliert, wenn die Protonenpumpe
als integrales Membranprotein vorliegt, wäre gemäss diesem Modell eine Aktivitätsveränderung der Protonenpumpe zu erwarten.
Im Abschnitt 3.5 wurde aber festgestellt, dass die Proteinkinase die Aktivität der Plasmamembran-H+-ATPase in Membranvesikeln nicht signifikant beeinflusst.
Eine Ursache für dieses Ergebnis könnte der Zustand der Plasmamembran-H+-ATPase vor der
Inkubation mit der GST-CDPK sein. Ist die H+-ATPase bereits zu diesem Zeitpunkt vollständig
phosphoryliert (z.B. durch das Fehlen cytosolischer Phosphatasen), ist eine Modulation der
Aktivität durch die Kinase nicht mehr möglich. Eine andere Erklärungsmöglichkeit wäre, dass
sich in den Vesikel-Membranen bereits viele membranintegrale oder Membran-assoziierte Kinasen befinden, welche die Plasmamembran-H+-ATPase während des Experimentes unabhängig von der exogenen GST-CDPK-Zugabe phosphorylieren können. Eine solche endogene Kinaseaktivität wurde bereits bei der in vitro-Phosphorylierung von Membranvesikeln aus Nicotiana plumbaginifolia in Gegenwart eines ATP- und Mg2+-haltigen Puffers, nicht aber einer exogen zugegebenen Proteinkinase festgestellt (Svennelid et al., 1999). Vielleicht liegt der CTerminus der Plasmamembran-integrierten H+-ATPase aber auch in räumlich anderer Konformation vor als der kurze, isolierte C-Terminus CT66. Dies hätte zur Folge, dass das Substrat
von der LeCPK1 evtl. nicht mehr erkannt und phosphoryliert werden könnte.
Es ist aber auch möglich, dass eine Phosphorylierung am C-Terminus der H+-ATPase tatsächlich stattfindet, ohne aber eine Aktivitätsveränderung zu bewirken. Eine Aktivierung setzt
nämlich gemäss Regulationsmodell zusätzlich zur Phosphorylierung die Bindung eines 14-3-3Protein-Dimers voraus (Morsomme und Boutry, 1999; Abb. 3 auf Seite 8). Die löslichen, cytoplasmatischen 14-3-3-Proteine sind aber in der gereinigten Membranvesikel-Suspension gar
nicht mehr vorhanden, was eine Aktivierung über diesen Mechanismus ausschliesst.
4. Diskussion
Seite 72
4.4 Die Rolle der LeCPK1 in pflanzlichen Abwehrreaktionen
Schon seit längerem ist bekannt, dass Elicitoren von pathogen Pilzen oder Bakterien die Aktivität der Plasmamembran-H+-ATPase modulieren können (Blum et al., 1988; Johansson et al.,
1993).
So bewirkte beispielsweise ein Elicitor aus Cladosporium fulvum eine Aktivierung der Protonenpumpe von Lycopersicon esculentum über eine Phosphatase-abhängige Dephosphorylierung
(Vera-Estrella et al., 1994). Ausserdem wurde gezeigt, dass bei Zugabe des pflanzlichen Peptidhormons Systemin das Wachstumsmedium von Lycopersicon peruvianum-Suspensionskulturzellen alkalisiert wird, was möglicherweise auf eine Deaktivierung der PlasmamembranH+-ATPase zurückzuführen ist (Schaller und Oecking, 1999). Eine Hemmung der H+-ATPase
mittels geeigneter Inhibitoren führt zu einer verstärkten Transkription mehrerer "systemic
wound response proteins" (SWRPs) in Tomatenpflanzen. Im Gegensatz dazu wurde die H+ATPase bei Zugabe von Fusicoccin aktiviert und das Wachstumsmedium dadurch angesäuert.
In Tomatenpflanzen unterdrückt Fusicoccin die Transkription der SWRPs. Anstelle der SWRPs
wurden andere, "pathogenesis-related" (PR)-Proteine verstärkt transkribiert (Schaller und Oekking, 1999). Diese unterschiedliche Regulation der H+-ATPase stellt offenbar eine differenzierte Antwort auf verschiedene, pathogene Umwelteinflüsse dar.
Da für die Modulation der H+-ATPase-Aktivität in einigen Fällen eine Ca2+-abhängige Phosphorylierung notwendig ist (Schaller und Sussman, 1988; Lino et al., 1998; Camoni et al.,
1998), stellt sich die Frage, ob die untersuchte LeCPK1 an einer der oben erwähnten Signaltransduktionen beteiligt sein könnte.
Die oben erwähnte Plasmamembran-H+-ATPase aus Lycopersicon esculentum, die nach Einwirkung eines Elicitors von Cladosporium fulvum durch eine Phosphatase dephosphoryliert und
aktiviert wurde (Vera-Estrella et al., 1994), wurde 30 min später durch zwei Ca2+-abhängige
Phosphorylierungen wieder rephosphoryliert, was die ursprüngliche H+-ATPase-Aktivität wieder herstellte (Xing et al., 1996). Bei den beiden beteiligten Proteinkinasen handelte es sich
aber wahrscheinlich nicht um CDPKs, sondern um eine Proteinkinase C und eine Ca2+/CaMKinase II (Xing et al., 1996). Auf der anderen Seite wird die Systemin-induzierte Alkalisierungsreaktion in Zellkulturen von Lycopersicon peruvianum durch die ProteinkinaseInhibitoren K-252a und Staurosporin unterdrückt (Schaller und Oecking, 1999). Die gleichen
4. Diskussion
Seite 73
Inhibitoren hemmen auch die in vitro-Phosphorylierung des C-Terminus der Protonenpumpe
(siehe Abschnitt 3.4), was auf die Beteiligung einer CDPK im Wundsignaltransduktionsweg
hinweist. Auch die Aktivierung einer bisher unbekannten CDPK durch den Avr9-Elicitor von
Cladosporium fulvum in Suspensionskulturzellen von Nicotiana tabacum weist auf eine Rolle
von CDPKs in pflanzlichen Abwehrreaktionen hin (Romeis et al., 2000). Zudem wurde in
Blättern von Zea mays unmittelbar nach Applikation von verschiedenen pilzlichen Elicitoren
oder der Infektion durch die Pilze selbst die Transkription einer spezifischen CDPK-Isoform
aktiviert (Murillo et al., 2001). Die Zunahme der CDPK-Transkripte war jeweils begleitet von
der Akkumulation eines für Zea mays typischen PR-Proteins. Bemerkenswert ist, dass sich das
differenzielle Expressionsmuster der CDPK und dasjenige des PR-Proteins im Verlaufe der
Infektion stark glichen.
Auch die hier untersuchte LeCPK1 erfüllt wichtige Bedingungen, die für die Beteiligung an der
Signaltransduktion als Antwort auf eine pathogene Infektion oder Verwundung notwendig sind.
So wurde gezeigt, dass die LeCPK1 durch eine Ca2+-Konzentration, wie sie in der lebenden
Zelle auftreten kann, aktiviert wird (siehe Abschnitt 3.9). Zudem befindet sie sich in vivo durch
Lokalisation an der Plasmamembran in der Nähe der H+-ATPase (siehe Abschnitte 3.7 und
3.8). Ferner kann die LeCPK1 in vitro den C-Terminus der Plasmamembran-H+-ATPase phosphorylieren (siehe Abschnitte 3.2 bis 3.4). Ausserdem weist die erhöhte Transkription der Proteinkinase nach Fusicoccin-Behandlung auf eine mögliche Funktion der LeCPK1 in der Abwehrreaktion der Tomatenpflanze hin (Stalder, 2000).
So könnte die Plasmamembran-H+-ATPase nach einer pilzlichen Infektion durch die Proteinkinase phosphoryliert und aktiviert werden. Die LeCPK1 könnte aber auch eine Rolle in der Systemin-induzierten Wundantwort spielen und die H+-ATPase durch Phosphorylierung inaktivieren. Gegen diese Möglichkeit spricht allerdings, dass nach Verwundung von Tomatenblättern
keine erhöhte LeCPK1-Transkription festgestellt werden konnte. Ausserdem konnte im Rahmen der vorliegenden Arbeit weder eine Aktivierung noch eine Inaktivierung der Plasmamembran-H+-ATPase durch die LeCPK1 nachgewiesen werden (siehe Abschnitt 3.5). In weiterführenden Studien könnte dieser Nachweis in Gegenwart von 14-3-3-Proteinen vielleicht doch
noch erbracht werden. Auch das Aufspüren weiterer LeCPK1-Substrate mittels der "yeast-twohybrid"-Methode könnte zu einer Aufklärung der Funktion der LeCPK1 beitragen.
5. Referenzen
Seite 74
V. LITERATUR
Abo-El-Saad, M. and Wu, R. (1995): A rice membrane calcium-dependent protein-kinase is induced by
gibberellin. Plant Physiol 108: 787-93.
Alberts, B., Bray, D., Lewis, J., Raff, M., Roberts, K. and Watson, J. D.: Molecular Biology of the Cell,
3rd edition. New York: Garland Publishing; 1994.
Ames, J. B., Ishima, R., Tanaka, T., Gordon, J. I., Stryer, L. and Ikura, M. (1997): Molecular mechanics
of calcium-myristoyl switches. Nature 389: 198-202.
Auer, M., Scarborough, G. A. and Kuhlbrandt, W. (1998): Three-dimensional map of the plasma membrane H+-ATPase in the open conformation. Nature 392: 840-3.
Babu, Y. S., Sack, J. S., Greenhough, T. J., Bugg, C. E., Means, A. R. and Cook, W. J. (1985): Threedimensional structure of calmodulin. Nature 315: 37-40.
Baizabal-Aguirre, V. M. and de la Vara, L. E. G. (1997): Purification and characterization of a calciumregulated protein kinase from beet root (Beta vulgaris) plasma membranes. Phys Plant 99: 135-43.
Bhatnagar, R. S. and Gordeon, J. I. (1997): Understanding covalent modifications of proteins by lipids:
where cell biology and biophysics mingle. Trends Cell Biol. 7: 14-20.
Binder, B. M., Harper, J. F. and Sussman, M. R. (1994): Characterization of an Arabidopsis calmodulinlike domain protein kinase purified from Escherichia coli using an affinity sandwich technique. Biochemistry 33: 2033-41.
Birnboim, H. C. and Doly, S. (1979): A rapid alkaline extraction procedure for screening recombinant
plasmid DNA. Nucl. Acids Res. 7: 1513-9.
Blum, W., Key, G. and Weiler, E. W. (1988): ATPase activity in Plasmalemma-rich vesicles isolated by
aqueous 2-phase partitioning from Vicia faba mesophyll and epidermis - characterization and influence
of abscisic-acid and fusicoccin. Phys Plant 72: 279-87.
Bowman, B. J., Berenski, C. J. and Jung, C. Y. (1985): Size of the plasma membrane H+-ATPase from
Neurospora crassa determined by radiation inactivation and comparison with the sarcoplasmic reticulum Ca2+-ATPase from skeletal muscle. J Biol Chem 260: 8726-30.
Buchanan, B. B., Gruissem, W. and Jones, R. L.: Biochemistry & Molecular Biology of Plants, 1st edition. Rockville, Maryland: American Society of Plant Physiologists; 2000.
Busconi, L. and Michel, T. (1993): Endothelial nitric oxide synthase membrane targeting. N-terminal
myristoylation determines subcellular localization. J Biol Chem 268: 8410-3.
Camoni, L., Fullone, M. R., Marra, M. and Aducci, P. (1998): The plasma membrane H+-ATPase from
maize roots is phosphorylated in the C-terminal domain by a calcium-dependent protein kinase. Phys
Plant 104: 549-55.
Camoni, L., Iori, V., Marra, M. and Aducci, P. (2000): Phosphorylation-dependent interaction between
plant plasma membrane H+-ATPase and 14-3-3 proteins. J Biol Chem 275: 9919-23.
Casey, P. (1995): Protein lipidation in cell signaling. Science 268: 221-5.
5. Referenzen
Seite 75
Chalfie, M. and Tu, Y. (1994): Green fluorescent protein as a marker for gene expression. Science 263:
802-5.
Chaudhuri, S., Seal, A. and Gupta, M. D. (1999): Autophosphorylation-dependent activation of a calcium-dependent protein kinase from groundnut. Plant Physiol 120: 859-66.
Cosgrove, D. J. (1997): Assembly and enlargement of the primary cell wall in plants. Annu Rev Cell
Dev Biol 13: 171-201.
Cubitt, A. B., Heim, R., Adams, S. R., Boyd, A. E., Gross, L. A. and Tsien, R. Y. (1995): Understanding, improving and using green fluorescent proteins. Trends Biochem Sci 20: 448-55.
Dambly, S. and Boutry, M. (2001): The two major plant plasma membrane H+-ATPases display different regulatory properties. J Biol Chem 276: 7017-22.
Degtyarev, M. Y., Spiegel, A. M. and Jones, T. L. Z. (1994): Palmitoylation of a G-Protein alpha(I)
subunit requires membrane localization but not myristoylation. J Biol Chem 269: 30898-903.
Desbrosses, G., Stelling, J. and Renaudin, J. P. (1998): Dephosphorylation activates the purified plant
plasma membrane H+-ATPase - possible function of phosphothreonine residues in a mechanism not
involving the regulatory C-terminal domain of the enzyme. Eur J Biochem 251: 496-503.
Douglas, P., Moorhead, G., Hong, Y., Morrice, N. and MacKintosh, C. (1998): Purification of a nitrate
reductase kinase from Spinacea oleracea leaves, and its identification as a calmodulin-domain protein
kinase. Planta 206: 435-42.
Ellard-Ivey, M., Hopkins, R. B., White, T. J. and Lomax, T. L. (1999): Cloning, expression and Nterminal myristoylation of CpCPK1, a calcium- dependent protein kinase from zucchini (Cucurbita
pepo L.). Plant Mol Biol 39: 199-208.
Finnie, C., Borch, J. and Collinge, D. B. (1999): 14-3-3 proteins: eukaryotic regulatory proteins with
many functions. Plant Mol Biol 40: 545-54.
Frick, U. (2001): Zielgerichtete Mutagenese einer CDPK aus Lycopersicon esculentum. Semesterarbeit
ETH Zürich
Fuglsang, A. T., Visconti, S., Drumm, K., Jahn, T., Stensballe, A., Mattei, B., Jensen, O. N., Aducci, P.
and Palmgren, M. G. (1999): Binding of 14-3-3 protein to the plasma membrane H+-ATPase AHA2
involves the three C-terminal residues Tyr946-Thr-Val and requires phosphorylation of Thr947. J Biol
Chem 274: 36774-80.
Gilli, R., Lafitte, D., Lopez, C., Kilhoffer, M.-C., Makarov, A., Briand, C. and Haiech, J. (1998): Thermodynamic Analysis of Calcium and Magnesium Binding to Calmodulin. Biochemistry 37: 5450-6.
Godsel, L. M. and Engman, D. M. (1999): Flagellar protein localization mediated by a calciummyristoyl/palmitoyl switch mechanism. EMBO J 18: 2057-65.
Gomes, E., Venema, K., Simon-Plas, F., Milat, M. L., Palmgren, M. G. and Blein, J. P. (1996): Activation of the plant plasma membrane H+-ATPase. Is there a direct interaction between lysophosphatidylcholine and the C-terminal part of the enzyme? FEBS Lett 398: 48-52.
Goormaghtigh, E., Chadwick, C. and Scarborough, G. A. (1986): Monomers of the Neurospora plasma
membrane H+-ATPase catalyze efficient proton translocation. J Biol Chem 261: 7466-71.
Görlach, J. and Schmid, J. (1996): Introducing StuI sites improves vectors for the expression of fusion
proteins with factor Xa cleavage sites. Gene 170: 145-6.
5. Referenzen
Seite 76
Harmon, A. C., Gribskov, M. and Harper, J. F. (2000): CDPKs - a kinase for every Ca2+ signal? Trends
Plant Sci 5: 154-9.
Harmon, A. C., Yoo, B. C. and McCaffery, C. (1994): Pseudosubstrate inhibition of CDPK, a protein
kinase with a calmodulin-like domain. Biochemistry 33: 7278-87.
Heim, R., Cubitt, A. B. and Tsien, R. Y. (1995): Improved green fluorescence. Nature 373: 663-4.
Hong, Y., Takano, M., Liu, C. M., Gasch, A., Chye, M. L. and Chua, N. H. (1996): Expression of three
members of the calcium-dependent protein kinase gene family in Arabidopsis thaliana. Plant Mol Biol
30: 1259-75.
Huang, J. F., Teyton, L. and Harper, J. F. (1996): Activation of a Ca2+-dependent protein kinase involves intramolecular binding of a calmodulin-like regulatory domain. Biochemistry 35: 13222-30.
Hunter, T. and Plowman, G. D. (1997): The protein kinases of budding yeast: six score and more.
Trends Biochem Sci 22: 18-22.
Hutton, J. C. and Siddle, K.: Peptide Homone Secretion - A Practical Approach, 1st edition. Oxford,
UK: Oxford University Press; 1990.
Hwang, I., Harper, J. F., Liang, F. and Sze, H. (2000): Calmodulin activation of an endoplasmic reticulum-located calcium pump involves an interaction with the N-terminal autoinhibitory domain. Plant
Physiol 122: 157-68.
Hwang, I., Sze, H. and Harper, J. F. (2000): A calcium-dependent protein kinase can inhibit a calmodulin-stimulated Ca2+ pump (ACA2) located in the endoplasmic reticulum of Arabidopsis. Proc Natl Acad
Sci U S A 97: 6224-9.
Iwata, Y., Kuriyama, M., Nakakita, M., Kojima, H., Ohto, M. and Nakamura, K. (1998): Characterization of a calcium-dependent protein kinase of tobacco leaves that is associated with the plasma membrane
and is inducible by sucrose. Plant Cell Physiol 39: 1176-83.
Jahn, T., Fuglsang, A. T., Olsson, A., Bruntrup, I. M., Collinge, D. B., Volkmann, D., Sommarin, M.,
Palmgren, M. G. and Larsson, C. (1997): The 14-3-3 protein interacts directly with the C-terminal region of the plant plasma membrane H+-ATPase. Plant Cell 9: 1805-14.
Johansson, F., Sommarin, M. and Larsson, C. (1993): Fusicoccin activates the plasma membrane H+ATPase by a mechanism involving the C-terminal inhibitory domain. Plant Cell 5: 321-7.
Johnson, D. R. (1994): Genetic and biochemical studies of protein N-myristoylation. Annu Rev Biochem
63: 869-914.
Johnson, K. D. and Chrispeels, M. J. (1992): Tonoplast-bound protein-kinase phosphorylates tonoplast
intrinsic protein. Plant Physiol 100: 1787-95.
Johnson, R. S., Ohguro, H., Palczewski, K., Hurley, J. B., Walsh, K. A. and Neubert, T. A. (1994): Heterogeneous N-acylation is a tissue- and species-specific posttranslational modification. J Biol Chem
269: 21067-71.
Kinoshita, T. and Shimazaki, K. (1999): Blue light activates the plasma membrane H+-ATPase by phosphorylation of the C-terminus in stomatal guard cells. EMBO J 18: 5548-58.
Klimczak, L. J. and Hind, G. (1990): Biochemical similarities between soluble and membrane-bound
calcium-dependent protein kinases of barley. Plant Physiol 92: 919-23.
5. Referenzen
Seite 77
Lanzetta, P. A., Alvarez, L. J., Reinach, P. S. and Candia, O. A. (1979): An Improved Assay for Nanomole Amounts of Inorganic Phosphate. Analytical Biochemistry 100: 95-7.
Lee, J. Y., Yoo, B. C. and Harmon, A. C. (1998): Kinetic and calcium-binding properties of three calcium-dependent protein kinase isoenzymes from soybean. Biochemistry 37: 6801-9.
Li, H. M., Dauwalder, M. and Roux, S. J. (1991): Partial-purification and characterization of a Ca2+dependent protein-kinase from pea nuclei. Plant Physiol 96: 720-7.
Lino, B., Baizabal-Aguirre, V. M. and Gonzalez de la Vara, L. E. (1998): The plasma-membrane H+ATPase from beet root is inhibited by a calcium-dependent phosphorylation. Planta 204: 352-9.
MacRobbie, E. A. (1998): Signal transduction and ion channels in guard cells. Phil Trans Royal Soc
353: 1475-88.
Martin, M. L. and Busconi, L. (2000): Membrane localization of a rice calcium-dependent protein kinase (CDPK) is mediated by myristoylation and palmitoylation. Plant J 24: 429-35.
Maudoux, O., Batoko, H., Oecking, C., Gevaert, K., Vandekerckhove, J., Boutry, M. and Morsomme, P.
(2000): A plant plasma membrane H+-ATPase expressed in yeast is activated by phosphorylation at its
penultimate residue and binding of 14-3-3 regulatory proteins in the absence of fusicoccin. J Biol Chem
275: 17762-70.
McMichael, R. W., Jr (1995): Spinach leaf sucrose-phosphate synthase and nitrate reductase are phosphorylated/inactivated by multiple protein kinases in vitro. Plant Physiol 108: 1077-82.
McMichael, R. W., Jr and Huber, S. C. (1995): Sucrose-Phosphate Synthase is inactivated by a Calcium-dependent Protein-Kinase. Plant Physiol 108: 142-.
Michelet, B. and Boutry, M. (1995): The Plasma Membrane H+-ATPase. Plant Physiol 108: 1-6.
Moorhead, G., Douglas, P., Cotelle, V., Harthill, J., Morrice, N., Meek, S., Deiting, U., Stitt, M., Scarabel, M., Aitken, A. and MacKintosh, C. (1999): Phosphorylation-dependent interactions between enzymes of plant metabolism and 14-3-3 proteins. Plant J 18: 1-12.
Moriau, L., Bogaerts, P., Jonniaux, J. L. and Boutry, M. (1993): Identification and characterization of a
second plasma membrane H+-ATPase gene subfamily in Nicotiana plumbaginifolia. Plant Mol Biol 21:
955-63.
Moriau, L., Michelet, B., Bogaerts, P., Lambert, L., Michel, A., Oufattole, M. and Boutry, M. (1999):
Expression analysis of two gene subfamilies encoding the plasma membrane H+-ATPase in Nicotiana
plumbaginifolia reveals the major transport functions of this enzyme. Plant J 19: 31-41.
Morsomme, P. and Boutry, M. (2000): The plant plasma membrane H+-ATPase: structure, function and
regulation. Biochim Biophys Acta 1465: 1-16.
Morsomme, P., Dambly, S., Maudoux, O. and Boutry, M. (1998): Single point mutations distributed in
10 soluble and membrane regions of the Nicotiana plumbaginifolia plasma membrane PMA2 H+ATPase activate the enzyme and modify the structure of the C-terminal region. J Biol Chem 273:
34837-42.
Morsomme, P., Slayman, C. W. and Goffeau, A. (2000): Mutagenic study of the structure, function and
biogenesis of the yeast plasma membrane H+-ATPase. Biochim Biophys Acta 1469: 133-57.
Mumby, S. M. (1997): Reversible palmitoylation of signaling proteins. Curr Opin Cell Biol 9: 148-54.
5. Referenzen
Seite 78
Murillo, I., Jaeck, E., Cordero, M. J. and San Segundo, B. (2001): Transcriptional activation of a maize
calcium-dependent protein-kinase gene in response to fungal elicitors and infection. Plant Mol Biol 45:
145-58.
Narvaez-Vasquez, J., Florin-Christensen, J. and Ryan, C. A. (1999): Positional specificity of a phospholipase A activity induced by wounding, systemin, and oligosaccharide elicitors in tomato leaves.
Plant Cell 11: 2249-60.
Nigg, E. A. (1997): Nucleocytoplasmic transport: signals, mechanisms and regulation. Nature 386: 77987.
Niu, X. M., Bressan, R. A., Hasegawa, P. M. and Pardo, J. M. (1995): Ion homeostasis in NaCl stress
environments. Plant Physiol 109: 735-42.
Oecking, C., Piotrowski, M., Hagemeier, J. and Hagemann, K. (1997): Topology and target interaction
of the fusicoccin-binding 14-3-3 homologs of Commelina communis. Plant J 12: 441-53.
Ohto, M. A. and Nakamura, K. (1995): Sugar-induced increase of calcium-dependent protein-kinases
associated with the plasma-membrane in leaf tissues of tobacco. Plant Physiol 109: 973-81.
Olsson, A., Svennelid, F., Ek, B., Sommarin, M. and Larsson, C. (1998): A phosphothreonine residue at
the C-terminal end of the plasma membrane H+-ATPase is protected by fusicoccin-induced 14-3-3 binding. Plant Physiol 118: 551-5.
Palmgren, M. G. and Axelsen, K. B. (1998): Evolution of P-type ATPases. Biochim Biophys Acta 1365:
37-45.
Palmgren, M. G. and Christensen, G. (1993): Complementation in situ of the yeast plasma membrane
H+-ATPase gene pma1 by an H+-ATPase gene from a heterologous species. FEBS Lett 317: 216-22.
Palmgren, M. G., Larsson, C. and Sommarin, M. (1990): Proteolytic activation of the plant plasma
membrane H+-ATPase by removal of a terminal segment. J Biol Chem 265: 13423-6.
Palmgren, M. G., Sommarin, M., Serrano, R. and Larsson, C. (1991): Identification of an autoinhibitory
domain in the C-terminal region of the plant plasma membrane H+-ATPase. J Biol Chem 266: 20470-5.
Pardo, J. P. and Slayman, C. W. (1988): The fluorescein isothiocyanate-binding site of the plasmamembrane H+- ATPase of Neurospora crassa. J Biol Chem 263: 18664-8.
Patharkar, O. R. and Cushman, J. C. (2000): A stress-induced calcium-dependent protein kinase from
Mesembryanthemum crystallinum phophorylates a two component pseudo-response regulator. Plant J
24: 679-91.
Pedchenko, V. K., Nasirova, G. F. and Palladina, T. A. (1990): Lysophosphatidylcholine specifically
stimulates plasma membrane H+- ATPase from corn roots. FEBS Lett 275: 205-8.
Pei, Z. M., Ward, J. M., Harper, J. F. and Schroeder, J. I. (1996): A novel chloride channel in Vicia faba
guard cell vacuoles activated by the serine/threonine kinase, CDPK. EMBO J 15: 6564-74.
Peitzsch, R. M. and McLaughlin, S. (1993): Binding of acylated peptides and fatty acids to phospholipid
vesicles: pertinence to myristoylated proteins. Biochemistry 32: 10436-43.
Portillo, F. (2000): Regulation of plasma membrane H+-ATPase in fungi and plants. Biochim Biophys
Acta 1469: 31-42.
5. Referenzen
Seite 79
Resh, M. D. (1994): Myristoylation and palmitoylation of Src family members: the fats of the matter.
Cell 76: 411-3.
Resh, M. D. (1999): Fatty acylation of proteins: new insights into membrane targeting of myristoylated
and palmitoylated proteins. Biochim Biophys Acta 1451: 1-16.
Roberts, D. M. and Harmon, A. C. (1992): Targets of intracellular calcium signals in higher plants. Annu Rev Plant Physiol Plant Mol Biol 43: 375-414.
Rodriguez-Concepcion, M., Yalovsky, S. and Gruissem, W. (1999): Protein prenylation in plants: old
friends and new targets. Plant Mol Biol 39: 865-70.
Romeis, T., Piedras, P. and Jones, J. D. (2000): Resistance gene-dependent activation of a calciumdependent protein kinase in the plant defense response. Plant Cell 12: 803-16.
Russell, J. D., Bhatnager, R. S., Knoll, L. J. and Gordon, J. I. (1994): Genetic and biochemical studies
of protein N-myristoylation. Annu Rev Biochem 63: 869-914.
Sambrook, J., Fritsch, E. F. and Maniatis, T.: Molecular cloning. A laboratory manual., 2nd edition.
New York: Cold Spring Harbor Laboratory Press; 1989.
Sanger, F., Nicklen, S. and Coulson, A. R. (1977): DNA-sequencing with chain-termination inhibitors.
Proc Natl Acad Sci U S A 74: 5463-7.
Satterlee, J. S. and Sussman, M. R. (1998): Unusual membrane-associated protein kinases in higher
plants. J Membr Biol 164: 205-13.
Schägger, H. and von Jagow, G. (1987): Tricine-sodium dodecyl sulfate-polyacrylamide gel electrophoresis for the separation of proteins in the range from 1 to 100 kDa. Anal Biochem 166: 368-79.
Schaller, A. (1999): Oligopeptide signalling and the action of systemin. Plant Mol Biol 40: 763-9.
Schaller, A. and Oecking, C. (1999): Modulation of plasma membrane H+-ATPase activity differentially
activates wound and pathogen defense responses in tomato plants. Plant Cell 11: 263-72.
Schaller, G. E., Harmon, A. C. and Sussman, M. R. (1992): Characterization of a calcium- and lipiddependent protein kinase associated with the plasma membrane of oat. Biochemistry 31: 1721-7.
Schaller, G. E. and Sussman, M. R. (1988): Phosphorylation of the plasma-membrane H+-ATPase of oat
roots by a calcium-stimulated protein-kinase. Planta 173: 509-18.
Scott, A., Wyatt, S., Tsou, P.-L., Robertson, D. and Strömgren Allen, N. (1999): Model System for
Plant Cell Biology: GFP Imaging in Living Onion Epidermal Cells. BioTechniques 26: 1125-32.
Shahinian, S. and Silvius, J. R. (1995): Doubly-lipid modified protein sequence motifs exhibit longlived anchorage to lipid bilayer membranes. Biochemistry 34: 3813-22.
Stalder, U. G. (2000): Eine Calciumabhängige Proteinkinase aus Lycopersicon esculentum: Klonierung,
Expression und Charakterisierung. Diplomarbeit ETH Zürich
Stone, J. M. and Walker, J. C. (1995): Plant protein kinase families and signal transduction. Plant Physiol 108: 451-7.
Svennelid, F., Olsson, A., Piotrowski, M., Rosenquist, M., Ottman, C., Larsson, C., Oecking, C. and
Sommarin, M. (1999): Phosphorylation of Thr-948 at the C-Terminus of the Plasma Membrane H+ATPase Creates a Binding Site for the Regulatory 14-3-3 Protein. Plant Cell 11: 2379-92.
5. Referenzen
Seite 80
Taiz, L. and Zeiger, E.: Plant Physiology, 2nd edition. Sunderland, MA: Sinauer Associates, Inc.; 1998.
Towler, D. A., Adams, S. P., Eubanks, S. R., Towery, D. S., Jackson-Machelski, E., Glaser, L. and Gordon, J. I. (1987): Purification and characterization of yeast myristoyl CoA:protein N- myristoyltransferase. Proc Natl Acad Sci U S A 84: 2708-12.
Towler, D. A., Eubanks, S. R., Towery, D. S., Adams, S. P. and Glaser, L. (1987): Amino-terminal
processing of proteins by N-myristoylation. Substrate specificity of N-myristoyl transferase. J Biol
Chem 262: 1030-6.
Towler, D. A., Gordon, J. I., Adams, S. P. and Glaser, L. (1988): The biology and enzymology of eukaryotic protein acylation. Annu Rev Biochem 57: 69-99.
Vara, F. and Serrano, R. (1982): Partial purification and properties of the proton-translocating ATPase
of plant plasma membranes. J Biol Chem 257: 12826-30.
Vera-Estrella, R., Barkla, B. J., Higgins, V. J. and Blumwald, E. (1994): Plant defense to fungal pathogens. Activation of host-plasma membrane H+-ATPase by elicitor-induced enzyme. Plant Physiol 104:
209-15.
Verhey, S. D., Gaiser, J. C. and Lomax, T. L. (1993): Protein-kinases in zucchini - characterization of
calcium-requiring plasma-membrane kinases. Plant Physiol 103: 413-9.
Wach, A., Supply, P., Dufour, J. P. and Goffeau, A. (1996): Amino acid replacements at seven different
histidines in the yeast plasma membrane H+-ATPase reveal critical positions at His285 and His701.
Biochemistry 35: 883-90.
Ward, J. M., Kuhn, C., Tegeder, M. and Frommer, W. B. (1998): Sucrose transport in higher plants. Int
Rev Cytol 178: 41-71.
Weaver, C. D., Crombie, B., Stacey, G. and Roberts, D. M. (1991): Calcium-dependent phosphorylation
of symbiosome membrane-proteins from nitrogen-fixing soybean nodules - evidence for phosphorylation of nodulin-26. Plant Physiol 95: 222-7.
Xing, T., Higgins, J. and Blumwald, E. (1996): Regulation of plant defense response to fungal pathogens: two types of protein kinases in the reversible phosphorylation of the host plasma membrane. Plant
Cell 8: 555-64.
Yalovsky, S., Rodriguez-Concepcion, M. and Gruissem, W. (1999): Lipid modifications of proteins slipping in and out of membranes. Trends Plant Sci 4: 439-45.
Yoo, B. C. and Harmon, A. C. (1996): Intramolecular binding contributes to the activation of CDPK, a
protein kinase with a calmodulin-like domain. Biochemistry 35: 12029-37.
Yoon, G. M., Cho, H. S., Ha, H. J., Liu, J. R. and Lee, H. S. (1999): Characterization of NtCDPK1, a
calcium-dependent protein kinase gene in Nicotiana tabacum, and the activity of its encoded protein.
Plant Mol Biol 39: 991-1001.
Zhang, F. L. and Casey, P. J. (1996): Protein prenylation: molecular mechanisms and functional consequences. Annu Rev Biochem 65: 241-69.
Zhao, Y., Pokutta, S., Maurer, P., Lindt, M., Franklin, R. M. and Kappes, B. (1994): Calcium-binding
properties of a calcium-dependent protein kinase from Plasmodium falciparum and the significance of
individual calcium-binding sites for kinase activation. Biochemistry 33: 3714-21.
6. Anhang
Seite 81
VI. ANHANG
6.1 Sequenz der LeCPK1-cDNA
1
GGCAAGTGGG GAAAAAGCCT AGAAAAATAA CAAGGGCAAA AGCTGGCAAA
51
GAAAGTGTGT AGCATTTTCA TGGAGTTTTT TCCCATGAAG TCAATGAAGA
101
GGGTTCAAAA CGTTGGCATT TTCTGATCTG TGGAATATCT TTTAGGTTGT
151
TGTTTTTTTT GTAACTTGTT GAGGAATTGA AGTATCCAAA GTTCAATCTT
201
GTTGAATAGA CTGTAGAAAT GGGTGGTTGT TTTAGCAAGA AGTATACCCA
251
ACAAGATGCT AATGGGCATA GGGCAGGAAG AAGAGTTAAT CAAGCATATC
301
AAAAACCACC ACAACCCCAG CCAGAAAGGC CATATCAGCC TCAGCCCCAG
351
CAGGAAAGGC CATATCAGCC ACCGCCACAG CCAGCATATC AGCCACCGCC
401
ACAGCCAAAG CCACAACCTC AGCCCCACCC TGTTCCTGTT ACTGTGCAGT
451
CTGGACAGCC CCAAGACCAA ATGCAAGGAC CCCATATGAA TAACATATTG
501
GGAAAGCCTT TTGAGGAAAT TAGAAAGCTC TATACACTTG GGAAAGAATT
551
GGGTAGGGGT CAGTTTGGAG TGACTTACTA TTGTACTGAG AACTCAACTG
601
GGAACCCTTA TGCTTGCAAG TCCATACTTA AGAGGAAGCT TGTAAGCAAG
651
AATGATAGGG AGGATATGAA GAGGGAAATT CAGATTATGC AGCATTTGAG
701
TGGGCAGCCA AACATTGTGG AATTCAAGGG TGCTTATGAA GATAGGCAGT
751
CAGTACACCT TGTGATGGAA CTTTGTGCTG GAGGAGAGTT GTTTGACAGG
801
ATTATCGCCC GTGGATATTA CTCAGAGAAG GATGCTGCTG AGATTATTAG
851
ACAGATTGTA AATGTTGTTA ACATTTGCCA TTTCATGGGT GTCATGCATA
901
GGGATCTCAA GCCAGAGAAT TTCTTACTGA CTAGTAAGGA TGAAAATGCT
951
ATGTTGAAGG CAACTGATTT TGGACTTTCT GTCTTCATTG AAGAAGGGAA
1001
GGTGTACCGT GATATAGTTG GTAGTGCATA TTATGTTGCC CCTGAAGTGT
1051
TGCGGCGTAG TTATGGGAAG GAAGCAGATG TATGGAGTGC AGGTGTTATT
1101
TTGTATATTC TGCTCAGTGG TGTACCTCCA TTTTGGGCTG AAACTGAAAA
1151
GGGAATATTT AATACCATAC TAAAAGGAGA AATTGACTTC CAAAGTGATC
1201
CATGGCCATC AATATCAAAT AGTGCCAAGG ACCTTATTCG GAAAATGCTA
1251
ACGCAGGAGC CAAGGAAGAG AATTACTTCC GCGCAAGTTC TTGAACATCC
6. Anhang
Seite 82
1301
ATGGCTTCGA CTTGGAGAAG CATCAGATAA GCCAATAGAC AGTGCAGTCC
1351
TGTCCAGAAT GAAGCAGTTC AGAGCAATGA ACAAGCTCAA AAAACTCGCA
1401
TTGAAGGTCA TTGCGGAAAA TTTATCTGAA GAAGAAATCA AGGGTCTGAA
1451
AGCTATGTTT CACAACATTG ATACGGACAA TAGTGGCACA ATCACTTATG
1501
AAGAACTGAA GTCGGGATTG GCTCGGCTTG GATCAAAGCT AACGGAGACT
1551
GAAGTCAAGC AACTCATGGA AGCTGCTGAT GTGGATGGAA ATGGATCAAT
1601
TGATTACATT GAGTTTATTA CTGCAACGAT GCATAGACAT CGGCTAGAAA
1651
GGGATGAGCA TCTTTTTAAA GCTTTTCAGC ATTTTGACAA GGACCATAGT
1701
GGATTCATCA CGCGAGATGA ATTGGAAAAC GCTATGAAGG AATATGGTAT
1751
GGGTGATGAG GCCACCATCA AGGAGATAAT CGCAGAGGTG GACACTGACA
1801
ATGACGGTAG GATCAATTAC GAGGAGTTCT GTGCTATGAT GAGAAGTGGA
1851
ACAACACAAC CACAACAAAA GCTTTTCTAG TGCATCGAGA GCAAATTACC
1901
CTTGCAACGA GCAGAGAACG TTCACCAGCC AGCACGATGG AGAGATGTCT
1951
ATCACGAGAG GATCAGTAAC TTAACATACT TCCATATTTC TTCAATCCTT
2001
CAGCTATCTT CAAAAAGCAC TGGAGTACAT GAGACCTTTT TCGTGTAGGT
2051
TGAGTTCGCG TGGAAAATGT GTGTATAGCT AGTTAATGGT ATATTTCGAG
2101
TTTCTTGTAA TGTATTTGAT CCCCCTTCGT AATTTTGTGT GGATCGCGTT
2151
GTGAAGTTGA CCTCCCGTAG AGATTATAAC AAGACAATCT GAATATAGCT
2201
TTATGCTTGA AAAAAAAAAA AAAAAAAAA
Abb. 28: Die cDNA-Sequenz der LeCPK1 aus Lycopersicon esculentum cv. Castelmart II.
Das Open Reading Frame (ORF) beginnt mit dem Startcodon für Methionin an Position 219 und endet mit dem
Stopcodon an Position 1880. Die Adeninbase an Position 1792 weicht ab von der ursprünglich durch Stalder
(2000) bestimmten Guaninbase.
6. Anhang
Seite 83
6.2 Standardkurve für die Aktivitätsbestimmung der Plasmamembran-H+-ATPase
2.5
E 660
2.0
1.5
y = 0.0877x - 0.0035
1.0
0.5
0.0
0
5
10
15
20
25
nmol Pi pro 100 µl Testansatz
Abb. 29: Standardkurve, die für die Bestimmung der freien Phosphatkonzentration bei der Aktivitätsmessung der
Plasmamembran-H+-ATPase verwendet wurde. Zur Berechnung der im Diagramm angegebenen Gleichung wurde
eine Regressionsgerade über die Resultate der Einzelmessungen gelegt.
DANK...
...gebührt vor allem Andreas Schaller, der mich mit viel Geduld und Humor in die Materie und
die praktische Arbeit im Labor einführte.
Auch Andreas Hiltbrunner, Roger Kuhn und Anne Samland sei herzlich gedankt für die Einführung in die Mikroprojektil-Transformationstechnik, die konfokale Mikroskopie und die Fluoreszenz-Spektrometrie.
Grossen Dank möchte ich auch David Frasson, Ursula Frick, Felix Hauser, Yoann Huet, Werner Schmidt und Jochen Strassner und allen anderen Mitgliedern der Arbeitsgruppe ausdrücken
für die überaus angenehme und freundliche Zusammenarbeit.
Zum Schluss möchte ich mich ganz herzlich bei Prof. Nikolaus Amrhein für seine grosszügige
Gastfreundschaft bedanken.
This document was created with Win2PDF available at http://www.daneprairie.com.
The unregistered version of Win2PDF is for evaluation or non-commercial use only.