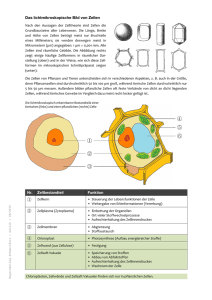
Vergleichende Analysen Antigen-beladener Nanopartikel mit UV
Werbung

Vergleichende Analysen Antigen-beladener Nanopartikel mit UVinaktivierten Kapsid-modifizierten Adenoviren in einem Proteinbasierenden Immunisierungs-Ansatz im Ovalbumin-Modell Dissertation zur Erlangung des Grades eines Doktors der Naturwissenschaften der Fakultät für Biologie und Biotechnologie an der Internationalen Graduiertenschule Biowissenschaften der Ruhr-Universität Bochum angefertigt in der Abteilung für Molekulare und Medizinische Virologie vorgelegt von Lena Johrden aus Essen Comparative anlysis of antigen-coated nanoparticles with UVinactivated capsid-modified adenovirus in a protein-based immunization approach in the ovalbumin model Dissertation to obtain the degree Doctor Rerum Naturalium (Dr. rer. nat) at the faculty of biology and biotechnology Ruhr-University Bochum International Graduate School of Biosciences Ruhr-University Bochum Department of Molecular and Medical Virology submitted by Lena Johrden from Essen, Germany Danksagung Als erstes möchte ich mich bei Herrn apl. Prof. Dr. med. O. Wildner für die Überlassung des Arbeitsplatzes, des Themas und seine Unterstützung bei der Umsetzung des Projektes bedanken. Zudem bedanke ich mich für die Bereitschaft die Betreuung der Arbeit aus der Ferne weiterzuführen. Bei Herrn Prof. Dr. G. A. Schaub bedanke ich mich herzlichst für die Übernahme der Zweitkorrektur dieser Arbeit. Herrn Prof. Dr. med. K. Überla danke ich dafür, dass ich meine Arbeit in seiner Arbeitsgruppe zu Ende führen durfte und er mir jederzeit für Fragen zur Verfügung stand. Der Arbeitsgruppe, bestehend aus Frau Dr. Wibke Bayer und Frau Dr. Ruth Lietz, danke ich für die nette Zeit, wobei ich einen besonderen Dank an Wibke für die gute Betreuung und Einführung in Methodik und Thematik aussprechen muss. Du hast mir besonders in der ersten Zeit sehr geholfen! Ein großer Dank gilt Dr. Matthias Tenbusch, und zwar nicht nur für die viele Geduld mit mir und für die zahlreichen Stunden, die er sich Zeit nahm, um mich in die Immunologie einzuführen, sondern auch für die fortwährende menschliche und moralische Unterstützung. Danke an Bettina, Bastian, Bianca, Michael und Torte, die mir besonders im Gedächtnis bleiben werden. Ich werde euch vermissen. Den restlichen Mitarbeitern der Abteilung aus MA (Alex, Sid, Nabi, Donatien, Klaus, Ulla, Regina, Heike, Andreia, Rosi, Uli und Martina) sowie dem ZKF (Sandra, Inga, Maik, Thomas, Andrea, Nadine), danke ich natürlich auch von Herzen für die liebe Aufnahme in die Abteilung und die unzähligen netten Stunden die wir zusammen hatten. Als Letztes möchte ich mich bei meiner Familie und meinen Freunden (Sara, Anni, Carmen, Kathrin, Anna und Hardy) bedanken. Ihr seid die Besten! Inhaltsverzeichnis 1 Einleitung 1 1.1 Induktion einer zellulären und humoralen Immunantwort 1 1.2 Immunisierungsstrategien 4 1.3 Adenoviren als Vektoren für Vakzinierungen 6 1.4 Nanopartikel 13 1.5 Zielsetzung 18 2 Material und Methoden 19 2.1 Material 19 2.1.1 Geräte und Verbrauchsmaterialien 19 2.1.2 Chemikalien und Lösungsmittel 20 2.1.3 Reagenzsysteme 23 2.1.4 Enzyme 24 2.1.5 Nährmedien 24 2.1.6 Puffer und Lösungen 25 2.1.7 Plasmide 30 2.1.8 Standards 30 2.1.9 Peptide 31 2.1.10 Antikörper und Tetramere 31 2.1.11 Bakterienstämme 32 2.1.12 Zelllinien 32 2.1.13 Polystyren Nanopartikel 33 2.1.14 Versuchstiere 33 2.2 Methoden 34 2.2.1 Molekularbiologische Arbeitsmethoden 34 2.2.1.1. Polymerasekettenreaktion 34 2.2.1.2. Agarose-Gelektrophorese und DNA-Elution 35 2.2.1.3. Restriktion von DNA und Ligation von DNA-Fragmenten 36 2.2.1.4. Transformation und Herstellung chemisch kompetenter Bakterien 37 2.2.1.5. Herstellung und Transformation elektrokompetenter Bakterien 38 2.2.1.6. Identifizierung rekombinanter Klone und Plasmid-Präparation 39 2.2.2 2.2.2.1. Proteinbiochemische Methoden Proteinexpression 40 40 2+ 2.2.2.2. Proteinaufreinigung über Ni -NTA-Säulen 40 2.2.2.3. Proteinbestimmung mittels der BCA Methode 40 2.2.2.4. Denaturierende Polyacrylamid-Gelelektrophorese 41 2.2.2.5. Western Blot 42 2.2.2.6. Kovalente Bindung von Proteinen an carboxylierte Polystyren- Nanopartikel 42 Zytologische Methoden 43 2.2.3.1. Kultivierung von Zelllinien 43 2.2.3.2. DNA-Transfektion von Zellen 44 2.2.3.3. Expressionsanalyse von Oberflächenproteinen mittels 2.2.3 Durchflusszytometrie 44 2.2.3.4. Virusproduktion, -anzucht, und -aufreinigung 45 2.2.3.5. Bestimmung der viralen und infektiösen Partikelzahl 45 2.2.3.6. UV-Inaktivierung von Adenoviren 46 2.2.3.7. Generierung von myeloiden Dendritischen Zellen aus Knochenmark-Vorläuferzellen 2.2.3.8. Nachweis der Aufnahme von Nanopartikeln durch Dendritische Zellen 2.2.3.9. 2.2.4 48 Nachweis Antigen-spezifischer T-Zell-Proliferation über einen CFSE-Verdünnnungsassay 2.2.3.11. 47 In vitro Aktivierung Dendritischer Zellen durch Antigen-beladene Nanopartikel und Adenoviren 2.2.3.10. 47 48 Inhibition der Aufnahmewege von Nanopartikeln und Adenoviren durch Dendritische Zellen 49 Immunologische Methoden 50 2.2.4.1. Immunisierung 50 2.2.4.2. In vivo Transport von Nanopartikeln 51 2.2.4.3. Blutentnahme 51 2.2.4.4. ELISA (Enzyme linked immunosorbent assay) 52 2.2.4.5. Isolierung von Lymphozyten aus der Milz 53 2.2.4.6. Intrazelluläre Zytokinfärbung (ICS) 53 2.2.4.7. Statistische Analyse 54 3 Ergebnisse 3.1 55 Beladung von Nanopartikeln unterschiedlicher Größe durch kovalente Bindung von Protein 55 3.2 Aufnahme von Nanopartikeln durch Dendritische Zellen in vitro 57 3.3 In vivo Transport von Nanopartikeln durch verschiedene Zell-Subtypen 3.4 60 Transgenexpression und Infektiösität von Adenoviren nach UV-Behandlung 3.5 61 Ergebnisse zur Aktivierung von Dendritischen Zellen durch die Aufnahme von Ova-beladenen Nanopartikeln, AdVpIX-OvapIX-Ova und UV-inaktiviertem AdVpIX-Ova 65 + 3.6 Ergebnisse der in vitro-Antigenpräsentation an CD8 Zellen durch Antigen-beladene Dendritische Zellen 3.7 68 Einfluss verschiedener Endozytose-Inhibitoren auf die zellulären Aufnahme von löslichem Protein, beladenen Nanopartikeln sowie Adenoviren 3.8 70 Einfluss der Proteinmenge auf die Immunantwort gegen lösliches Ova und Ova-beladene 93 nm Partikel 3.9 71 Ermittlung der geeigneten Applikationsroute für Antigen-beladene Nanopartikel 3.10 72 Vergleichende Analyse der Immunantwort nach Immunisierung mit löslichem Ovalbumin, Ovalbumin-beladenen Partikeln, AdVpIX-Ova und AdVpIX-OvapIX-Ova 3.11 75 Abhängigkeit der Antikörperproduktion und der Induktion zytotoxischer CD8 T-Zellen von der CD4+ T-Zellpopulation 80 4 Diskussion 83 5 Zusammenfassung 92 6 Abstract 93 7 Literatur 94 8 Dissertationsbezogene bibliographische Daten 113 9 Lebenslauf 114 Abbkürzungsverzeichnis Abb Abbildung AK Antikörper APS Ammoniumperoxydisulfat Ad5 Adenovirus Typ 5 AdV Adenovirus AIDS Aquired Immunodeficiency Syndrome APC Allophycocyanin BSA bovines Serum-Albumin bp Basenpaare bspw beispielsweise bzw beziehungsweise Ca Calcium CAR Coxsackie-Adenovirus-Rezeptor CFSE Carboxyfluoresceinsuccinimidylester CMV Cytomegalovirus CTL cytotoxische T-Lymphozyten DZ Dendritische Zellen DMSO Dimethylsulfoxid DNA Desoxyribonukleinsäure EDTA Ethylendiamintetraacetat ELISA Enzyme-Linked Immunosorbent Assay et al. und andere FCS fetales Kälberserum FITC Fluoresceinisothiocyanat FACS Durchflusszytometer (Fluorescence Activated Cell Sorting) Fc kristallisierbares Antikörperfragment (fragment cristallizable) g Erdbeschleunigung (gravity) HBV Hepatitis B Virus HIV Humanes Immundefizienzvirus HPV Humanes Papillomavirus HRP Horseradish-Peroxidase Hepes N-2-Hydroxyethylpiperazin-N-ethansulfonsäure Ig Immunglobulin i.m. intramuskulär i.p. intraperitoneal i.v. intravenös IL Interleukin Kb Kilobasen kDa Kilodalton MHC major histocompatibility complex MOI multiplicity of infection OD optische Dichte Ova Ovalbumin PBS Phosphat-gepufferte Saline PE Phycoerythrin RPMI Roswell Park Memorial Institute von 1960 RNA Ribonukleinsäure RT Raumtemperatur SDS Natriumdodecylsulfat TAE Tris-Acetat-EDTA TEMED N,N,N´,N´-Tetramethylethylendiamin Tris Tris-hydroxymethyl-aminomethan TLR Toll-like-Rezeptor Treg regulatorische T-Zelle U Einheiten (units) u.a. unter anderem UV Ultraviolett VP virale Partikel w/v Masse/Volumen z.B. zum Beispiel Einleitung 1 1 Einleitung 1.1 Induktion einer zellulären und humoralen Immunantwort Nach Eindringen eines Pathogens greift zunächst die angeborene Immunantwort (Abb. 1.1). Zum einen nehmen Makrophagen den Erreger auf und bauen diesen ab. Zum anderen werden bestimmte Muster des Pathogens, bspw. die Lipopolysaccharide der Zellmembran Gram-negativer Bakterien, von sogenannten PRRs (Pattern-Recognition-Receptors) erkannt. Diese werden von einer Vielzahl von Zellen exprimiert, unter anderem Dendritischen Zellen (DZ). Insbesondere Dendritische Zellen übernehmen mit ihrer Funktion als Antigen-präsentierende Zellen eine wichtige Rolle in der Induktion primärer Immunantworten. Sie verbinden somit die angeborene und adaptive Immunität [1, 2]. Unreife DZ aus dem Knochenmark wandern in peripheres Gewebe ein, wo sie für einen längeren Zeitraum verweilen. Tritt ein Antigen mit der Zelle in Kontakt, ist sie in der Lage, dieses über Pinozytose und Phagozytose aufzunehmen und anschließend über MHC-I- und II-Komplexe zu präsentieren [3-5]. Zudem exprimieren unreife Dendritische Zellen eine Reihe von internalisierenden Oberflächenproteinen, die bei Antigenkontakt zur rezeptorvermittelten Endozytose befähigt sind. Dazu zählen unter anderem C-Typ Lektin-Rezeptoren, wie der Makrophagen-Mannose-Rezeptor MMR, Dec205 sowie Fc-Rezeptoren des Typs Fcγ und Fcε, die eine Aufnahme von Immunkomplexen ermöglichen [6-8]. Erst die ausdifferenzierte Dendritische Zelle kann eine zelluläre Immunantwort auslösen. Die Reifung nach Antigenaufnahme erfolgt durch eine Vielzahl von Gefahrensignalen, die über Toll-like-Rezeptoren (TLRs) oder aber Turmor-NekroseFaktor-Rezeptoren vermittelt werden [9-11], und in einer phänotypischen sowie funktionellen Veränderung der Zelle resultieren. Insbesondere bakterielle Lipopolysaccharide (LPS) [8] und inflammatorische Zykokine wie TNFα eignen sich dazu [12, 13], Dendritische Zellen in vitro ausreifen zu lassen. Bei Ausbleiben dieser Gefahrensignale kann es dazu kommen, dass die Zelle in einen unreifen, Antigenpräsentierenden Zustand übergeht und so zu peripherer Toleranz führen kann. Nach der Reifung verlieren die Dendritischen Zellen ihre endozytotischen Fähigkeiten und präsentieren das aufgenommene Antigen verstärkt über MHC-I-Moleküle auf der Zelloberfläche [2, 14]. Zudem wird die Expression bestimmter kostimulatorischer Moleküle wie beispielsweise CD80, CD83, CD86, CD40 und auch MHC-I/II- Einleitung 2 Komplexe hochreguliert [14]. Zusätzlich werden verschiedene Zytokine wie IL-2, IFNγ und IL-12 sezerniert, die wiederum einen Einfluss auf die Aktivierung und Differenzierung von T-Zellen ausüben [15]. Dendritische Zellen sind die einzigen bisher bekannten Zellen, die naive T-Zellen stimulieren können, wobei dies vornehmlich in den lymphatischen T-Zell-Arealen geschieht, in die diese Zellen einwandern [16, 17]. Abb. 1.1: Schematische Darstellung des Immunsystems der Säugertiere Nach Eindringen eines Pathogens greift zunächt die angeborene Immunantwort, bei der es von Makrophagen abgebaut oder von anderen Antigen-präsentierenden Zellen über Endozytose, Pinozytose, TLRs (Toll-like-Rezeptoren) oder PRRs (Pattern-Recognition-receptors) aufgenommen wird. Die Zelle wandert in die sekundären lymphoiden Organe ein, sezerniert nach ihrer Aktivierung inflammatorische Zytokine und Interferone und präsentiert zudem das auf MHC-Komplexe geladene Antigen an naive T-Zellen. Die zur adaptiven Immunantwort zählenden CD4+ T-Zellen entwicklen sich in Abhängigkeit von dem umgebenden Zytokinmilieu zu CD4+ T-Zellen des Typs TH1 oder TH2. Während CD4+ T-Zellen des Typs TH1 eine CTL- (cytotoxic T lymphocyte) Antwort in Form von zytotoxischen CD8+ T-Zellen induzieren, werden durch TH2-Zellen B-Zellen aktiviert, die wiederum Antikörper gegen das invasive Pathogen produzieren. Modifiziert nach [18] Einleitung 3 Die Differenzierung von T-Lymphozyten zu zytotoxischen CD8+ T-Zellen erfolgt durch drei Signale. Zum einen erkennen die CD8+ Zellen mit Hilfe spezifischer T-ZellRezeptoren das über MHC-I-Komplexe präsentierte Antigen, zum anderen benötigen sie eine zusätzliche Stimulation durch B7-CD28 Interaktion, um in einen Effektorphänotyp zu differenzieren und zu proliferieren. Bei dem dritten Signal handelt es sich um das Vorhandensein bestimmter Zytokine [19-21]. Auch die Ausbildung einer T-Helferzell-Antwort durch CD4+ T-Lymphozyten spielt in diesem Zusammenhang eine wichtige Rolle. Diese sind in die Aktivierung von Antigen-spezifischen B-Zellen, Makrophagen und Dendritischen Zellen involviert, wobei das umgebende Zytokinmilieu einen Einfluss darauf nimmt, ob eine TH1- oder TH2-Antwort induziert wird [2123]. Während eine hohe Konzentration an IL-12 zu einem IFNγ-produzierenden CD4+ T-Zell-Phänotyp (T-Helferantwort Typ TH1) mit positivem Einfluss auf CTLs und Makrophagen führt [24, 25], differenzieren die Zellen in Gegenwart von IL-4 in einen T-Helfertyp der Subklasse TH2 [26], welcher der Aktivierung von Makrophagen entgegenwirkt. Im Falle viraler Infektionen ist der TH1-Immantwort-Typ dominant und bei bakteriellen Infektionen zumeist TH2. Neben der zellulären Reaktion spielen Antikörper-produzierende B-Zellen eine große Rolle bei der adaptiven Immunität, da sie langfristig den Schutz gegen Reinfektionen vermitteln [27]. B-Zellen enstehen aus hämatopoetischen Stammzellen der fötalen Leber bzw. des Knochenmarks. Im Gegensatz zu T-Zellen erkennen sie nicht nur Peptidfragmente, sondern ganze Proteine. Repetitive Strukturen können zu einer T-Zell-unabhängigen Aktivierung der B-Zellen führen, indem sich mehrere Immunoglobulin-Rezeptoren untereinander verlinken. Auch die direkte Präsentation von Antigenen durch DZ an B-Zellen ist hierbei möglich. Weitaus häufiger ist jedoch die T-Zell-abhängige Aktivierung der B-Zellen. Nach Kontakt eines Antigens mit einer durch die Lymphbahnen zirkulierenden B-Zelle wird dieses über B-Zellrezeptorvermittelte Endozytose internalisiert und auf MHC-II-Komplexen präsentiert. Anschließend wandert die Zelle in die sekundären lymphatischen Gewebe ein und trifft dort im parakortikalen Bereich auf Antigen-spezifische CD4+ T-Zellen, die eine TH2Antwort einleiten. Für die Aktivierung der B-Zelle sind nun 2 Signale notwendig. Zum einen interagiert sie mit dem T-Zell-Rezeptor der CD4+ T-Zelle, zum anderen kommt es zu einer kostimulatorischen Interaktion zwischen CD40 und dem Liganden CD40L, was wiederum die T-Zelle dazu anregt, den B-Zell-Wachstumsfaktor IL-4 auszuschütten [28]. Als Abschluss der folgenden klonalen Expansion entstehen Anti- Einleitung 4 körper-sezernierende Plasmazellen sowie -- im Falle der T-Zell abhängigen Aktivierung -- B-Gedächtniszellen. Ein weiteres Charakteristikum dieses Aktivierungsweges ist der Klassenwechsel. Während bei T-Zell unabhängigen Antigenen nur IgM und IgD gebildet wird, kommt es bei T-Zell abhängigen Antigenen im Keimzentrum zu einem Isotypwechsel, bei dem die Isotypen IgA sowie IgE aus IgG entstehen. Diese werden im Gegensatz zu IgM nicht in der akuten Phase ausgeschüttet, sondern sind erst etwa zwei Wochen nach Infektion detektierbar [29]. 1.2 Immunisierungsstrategien Trotz fortschreitender Erkenntnisse in der anti-viralen Therapie stellt die Entwicklung prophylaktischer und therapeutischer Impfstoffe, insbesondere gegen HIV, eine der wichtigsten Herausforderungen dar [30]. Die meisten der heute eingesetzten Vakzine induzieren neutralisierende Antikörper, die eine systemische Verbreitung des Pathogens verhindern sollen, und setzen zusätzlich auf die Induktion zellulärer Immunantworten. Klassische Impfstoffe, wie zum Beispiel gegen Masern, enthalten attenuierte Viren, die durch Mutationen in ihrer Replikation stark eingeschränkt sind. Trotz guter humoraler und zellulärer Antworten stellen sie jedoch aufgrund der möglichen mutationsbedingten Rückentwicklung und Wiederherstellung der Virulenz für manche Anwendungen zum Teil ein Sicherheitsrisiko dar [31, 32]. Wesentlich sicherer sind hingegen genetische Impfstoffe, die auf DNA-Immunisierungen oder rekombinanten viralen Vektoren basieren, jedoch befindet sich die Forschung noch in den Anfängen, und es sind noch keine dieser genetischen Vakzine zugelassen. Da gegen manche virale Infektionen, wie z.B. Hepatitis C und HIV, auch nach jahrelanger Forschung noch noch kein Impfstoff erfolgreich entwickelt wurde, ist ein Austesten innovativer Strategien erforderlich. Die intramuskuläre Injektion rekombinanter Plasmid-DNA führte zur Expression der verwendeten Reporterproteine, und diese blieben bis zu einem Jahr detektierbar [33-35]. Zudem wurden sowohl humorale als auch zelluläre Immunantworten gegen das endogen exprimierte Antigen nachgewiesen, und zwar im Mausmodell sowie in Rhesus-Makaken [35-39]. Große Vorteile von Plasmid-DNA stellen die Stabilität, die einfache und schnelle Produktion sowie die geringe Toxizität dar. Gleiches gilt auch für Protein-Impfstoffe, die jedoch kaum zytotoxische CD8+ T-Zellen induzieren können, da sie meist über MHC II-Komplexe präsentiert werden. In seltenen Fällen Einleitung 5 werden extrazelluläre Proteine auch von Antigen-präsentierenden Zellen aufgenommen und mittels cross-priming über MHC I präsentiert [19-21, 36, 37]. Schon seit längerer Zeit wird nach Möglichkeiten gesucht, die Immunantwort gegen die applizierten Antigene zu erhöhen, zum einen, um einen besseren Impfschutz zu erzielen, zum anderen, um die bei einer Impfung benötigte Antigenmenge zu reduzieren. Beispielsweise resultiert die Applikation von rekombinanten Proteinen nur in einer geringen Immunogenität. Bei den meisten eingesetzten Impfstoffen die auf Proteinen basieren, wie z. B. dem Impfstoff gegen Influenza A oder humanes Papillomavirus (HPV), wird die Immunantwort durch die Koapplikation von Adjuvantien erhöht [38, 39]. Die ältesten eingesetzten Adjuvantien sind komplettes Freund’sches Adjuvanz, eine Mineralöl-Wasser-Emulsion mit Mycobakterienextrakt, oder Alum, ein Aluminium-Hydroxygel [21, 37]. Beide erhöhen die Immunogenität des Antigens, indem sie dessen Freisetzung verlangsamen und die Expression von kostimulatorischen Molekülen durch Immunzellen erhöhen. Da sie jedoch teils heftige Entzündungsreaktionen und Gewebezerstörungen hervorrufen können, wird intensiv nach Alternativen geforscht. Im Gegensatz dazu bieten Toll-like-Rezeptor-Liganden eine gute Alternative, um kostimulatorische Signale zu vermitteln. Toll-Rezeptoren wurden erstmals in D. melanogaster identifiziert, später konnten diese zur Familie der PRRs (pattern recognition receptors) gehörenden Rezeptoren auch im Menschen nachgewiesen werden und erhielten dort den Namen Toll-like-Rezeptoren. Die neun TLRs unterscheiden sich in den erkannten Liganden. TLR3 bindet doppelsträngige RNA als Virus-assoziierte Struktur, wobei die synthetisch hergestellte RNA Polyriboinosin-Polyribocytidinsäure, kurz Poly(I :C) schon in diversen Studien erfolgreich als Adjuvanz getestet wurde [40-42]. Spezifische, unmethylierte DNA-Sequenzen mit CpG-Motifen stellen als Bakterien-assoziierte Komponenten die Liganden des TLR9 dar. Auch in diesem Fall wurden synthetisch hergestellte Oligodesoxynukleotide erfolgreich getestet [43-45]. Die Immunogenität kann auch dadurch gesteigert werden, dass das Antigen genetisch mit einem stimulatorischen Molekül fusioniert wird. Beispielsweise führte eine Fusion des Tumorantigens HER2/Neu an den Wachstumsfaktor GM-CSF, der an der Reifung Dendritischer Zellen beteiligt ist, zur Induktion einer erhöhten Immunantwort gegen HER2/Neu im Vergleich zu dem Antigen alleine [46]. Auch die Kopplung eines Antigens an Moleküle, die an Rezeptoren auf Antigen-präsentierenden Zellen binden, können die Immunogenität stei- Einleitung 6 gern, da das Antigen schneller aufgenommen und somit effektiver prozessiert und präsentiert werden kann [47, 48]. Auf der Suche nach anderen, möglichst effektiven Methoden zur Verbesserung der Immunogenität sind besonders modifizierte Pockenviren und adenovirale Vektoren in den Fokus geraten (siehe Abschnitt 1.3). Diese gelten als starke Stimulatoren des angeborenen Immunsystems und sollten sich somit positiv auf die Immunogenität des Impfstoffes auswirken [49]. Momentan sind Kombinationen aus DNA und rekombinanten Adenoviren unter genauerer Evaluierung in klinischen Studien, da diese im Affenmodell zu vielversprechenden Antigen-spezifischen Immunantworten führten [50, 51]. 1.3 Adenoviren als Vektoren für Vakzinierungen Adenoviren wurden erstmalig 1953 aus adenoiden Zellen des Rachenraumes isoliert [52]. Seither wurden über 100 verschiedene Adenovirus-Spezies aus Vögeln (Aviadenoviren), Reptilien (Atadenoviren), Amphibien (Siadenoviren) und Säugern (Mastadenoviren) identifiziert, die sich sowohl in ihrer Molekularbiologie als auch chemischen Zusammensetzung unterscheiden [53]. Die Klassifikation in die Subgruppen A bis F erfolgt dabei aufgrund mehrerer Charakteristika, u. a. dem onkogenen Potential in immunkompetenten Versuchstieren, der Fähigkeit zur Agglutination von Erythrozyten und Sequenzhomologien des viralen Genoms [3, 4]. Zurzeit sind 51 humane Adenovirus Serotypen bekannt, die sehr variable Krankheitsbilder hervorrufen. Während die Serotypen B1, C und E Entzündungen der Atemwege auslösen, führt eine Infektion mit den Serotypen B und D zu okularen Erkrankungen, mit B2 zu Nieren- und Urogenitalerkrankungen, und Serotyp F löst eine Gastroenteritis aus. Die Übertragung erfolgt meistens über kontaminierte Flüssigkeiten oder Aerosole. Bei immundefizienten Personen kann eine adenovirale Infektion in seltenen Fällen zum Tode führen [54, 55]. Adenoviren gehören zur Gruppe der nicht-umhüllten DNA-Viren (Abb. 1.2). Das 34-44 Kilobasenpaare lange, lineare Doppelstrang-Genom ist als DNA-Protein-KernKomplex von einem ikosahedrisch geformten Kapsid umschlossen. In EM- und Röntgenaufnahmen weist das Kapsid aller Adenoviren die gleiche Morphologie auf, wobei der sphärische Durchmesser 80-100 nm beträgt [56]. Insgesamt sieben der elf Strukturproteine formen das virale Kapsid, wobei die Proteine II (Hexon), III (Penton) und IV (Fiber) die Hauptbestandteile darstellen [57]. Einleitung 7 Die 240 Trimere des Hexon-Proteins, welches eines der ersten kristallographisch analysierten eukaryotischen Proteine darstellt, formen jede der 20 triangulären Seitenflächen des Kapsids und machen damit 63% der totalen Proteinmasse aus [58-60]. Die kristallographische Untersuchung belegte zudem, dass Adenoviren der gleichen evolutionären Linie wie der Bakteriophage PRD1 entstammen, da beide die gleiche Faltung des Hexons aufweisen. Anschließend haben sie sich in drei bis vier unabhängig voneinander entwickelnde Linien aufgeteilt [61]. Das Hexonprotein weist ein hohe Resistenz gegen physikochemische Einwirkungen auf, selbst 8 M Harnstoff wirken sich nicht aus das Hexon aus [62]. Core‐Protein (V) Lineares DNA‐Genom Fiber‐Protein (IV) Pentonbasisprotein (III) Protein IV Polypeptid IX (pIX) Protein VIII Terminales Protein Core‐Protein (VII) Hexon‐Protein (II) Abb. 1.2: Struktur des adenoviralen Virions Adenoviren besitzen ein nicht-umhülltes, ikosahedrales Kapsid, das aus den drei Proteinen Hexon, Pentonbasis und Fiber gebildet wird. Die doppelstränige DNA ist im Inneren eingeschlossen. Das Kapsid wird von mehreren Proteinen stabilisiert, insbesondere dem Polypeptid IX [zur Verfügung gestellt von Dr. W. Bayer]. An den 12 Ecken des Virions versiegelt das Protein III (Penton) das Kapsid. Es setzt sich aus der pentameren Penton-Basis und der trimeren Fiber (Protein IV) zusammen, die gemeinsam den Penton-Komplex bilden [57]. Die Fiber lässt sich in 3 Domänen unterteilen: der in die Penton-Basis eingelagerte, N-terminale Schwanz, eine zentrale Shaft-Region mit 15 Aminosäuren langen repetitiven Motiven und der C-terminalen globulären Kopf-Domäne [57, 58, 63]. Die Variation der Länge der Fiber zwischen den Serotypen liegt dabei in der verschiedenen Anzahl an Sequenzwiederholungen in der Shaft-Region begründet: während Ad2 und Ad5 je 22 Wiederholungen aufweisen, sind es nur sechs bei Adenovirus Typ 3 [64, 65], wobei stets Einleitung 8 das Aminosäuremotiv FNPVYPV zwischen den Serotypen hoch konserviert bleibt [54]. Neben der Eigenschaft als Stabilisierungselement des Kapsids dient der Fiberkopf hauptsächlich der ersten Kontaktaufnahme mit den Rezeptoren der Wirtszelle (Abb. 1.3). Bei den meisten Serotypen handelt es sich bei dem ersten Interaktionspartner um den Coxsackie-und-Adenovirus-Rezeptor CAR. Manche Serotypen wie zum Beispiel Ad35 interagieren jedoch mit dem Rezeptor CD46 [63]. Abb. 1.3: Internalisierung von Adenoviren Die primäre Bindung erfolgt an den Coxsackie- Rezeptor Clathrin‐umhüllte Einbuchtung Integrin Endozytose Endosom und-Adenovirus-Rezeptor anschließende (CAR). Interaktion mit Durch die zellulären Integrinen kommt es zur Clathrin-vermittelten Internalisierung des Virions. Nach Ansäuerung des Endosoms wird der kapsidäre Teil in das Cytoplasma entlassen und über Mikrotubuli zum Zellkern transportiert, wo die Transkription der viralen Gene erfolgt. Angesäuertes Endosom Bindung an nuklearen Kern‐Komplex Abbau des Kapsids DNA Transport in den Nukleus Für die im nächsten Schritt folgende Internalisierung interagiert ein zwischen den Subgruppen A, B, C und E stark konserviertes Arg-Gly-Asp (RGD-) Motiv in der variablen Region der Pentonbasis mit den zellulären Integrinen αVβ3 und α5β1. Einleitung 9 Dadurch sollen die Integrine aggregieren bzw. Cluster ausbilden und so das Signal für die Aktivierung des Integrin-vermittelten Signalwegs in Gang setzen. Dies führt zu einer Membranpermeabilisierung und anschließender Endozytose des gesamten Virions [57]. Indem das Endosom angesäuert wird, kommt es zur Lyse des endosomalen Vesikels, und der Viruspartikel wird in das Zytoplasma der Zelle entlassen. Anschließend interagieren die Hexonproteine mit Mikrotubuli, wodurch der Transport durch die nukleären Poren in den Nukleus ermöglicht wird. Dort findet anschließend die Transkription der viralen Gene statt, wobei diese in drei zeitliche Phasen unterteilt wird. Die frühen Gene, zu denen die Regionen E1-E4 gehören, verbessern die Virusreplikation und stimulieren zudem die Expression der intermediären und späten viralen Gene. Ein weiteres Protein mit stabilisierender Eigenschaft – eine Assemblierung ist zwar ohne dieses Protein möglich, das Virion ist jedoch wesentlich instabiler und thermosensitiver ̶ ist das 140 Aminosäuren umfassende Polypeptid IX (pIX). Aus diesem Grund wird es auch als Zementprotein bezeichnet [66]. Das für dieses Protein kodierende Gen besitzt einen eigenen Promotor; die Expression wird zu einem intermediären Zeitpunkt während der Infektion gestartet. Zunächst kommt pIX seiner Funktion als Transkriptionsaktivator der späten Gene nach und fördert weitergehend die Virusproliferation. Anschließend assoziiert pIX mit der „Gruppe-ausNeun“ Hexonen (Group-of-nine, GONs), wo pro Fläche je 4 zusammengelagerte Trimere in großen Vertiefungen zwischen den Hexonproteinen lokalisiert sind. Insgesamt sind 240 pIX-Moleküle pro Virion vorhanden [67, 68]. Eine Leucin-reiche Region im Carboxy-terminalen Ende ist für die Trimerisierung verantwortlich, wobei diese nicht zwingend für eine Virusassemblierung erforderlich ist [58, 66, 69]. Während der N-terminale Teil des Proteins zwischen den Hexonen verankert ist, ragt der C-terminale Teil zwischen diesen hervor und ist an der Oberfläche des Kapsids exponiert. Aus diesem Grund haben schon mehrere Forschergruppen erfolgreich verschiedene Proteine an das pIX fusioniert, um dem Viruspartikel zusätzliche Funktionen zu geben. Beispielsweise ist es mehreren Arbeitsgruppen gelungen, ein Fusionskonstrukt aus pIX und dem Reportergen GFP in das Virion einzubauen. Dadurch waren sie in der Lage, den Transport des Virus in Zellen sowie Geweben zu verfolgen [58, 67, 68]. Andere fusionierten das Reportergen Luciferase und pIX und belegten in mehreren Versuchen eine gleichbleibende Replikation, Transduktionsfähigkeit sowie Expression im Vergleich zu Wildtyp-Viren [70]. Eine Fusion mit einem Einleitung 10 Einzelkettenantikörper gegen β-Galaktosidase erhöhete die Transduktionseffizienz βGalaktosidase-exprimierender Zellen [71]. Auch für Vakzinierungszwecke wurde schon die Fusion eines Antigens an das pIX evaluiert. Die Vakzinierung mit einem adenoviralen Vektor, der ein Fusionsprotein aus pIX und dem Friend-Virus gp70Hüllprotein kodiert, wies einen positiven Effekt der zusätzlichen Präsentation des Antigens auf der Oberfläche des Virus auf die Immunantwort nach der Immunisierung auf. Dies äußerte sich in einer reduzierten Viruslast in der Milz nach Belastungsinfektion sowie in einem Anstieg Antigen-spezifischer Antikörper und TZellen im Vergleich zu dem nur pIX-gp70 exprimierenden Vektor [72]. Adenoviren werden des Weiteren schon seit geraumer Zeit als Gentransfervektoren eingesetzt, die nach der Methode von He et al. [73] in transkomplementierenden Produktionszellen, die die zur Replikation notwendigen Genprodukte in trans zur Verfügung stellen, hergestellt werden. Zu den Vorteilen zählen die Fähigkeit zur Transduktion von post-mitotischen Zellen mit einem breiten Zelltropismus, eine hohe Transduktionseffizienz, die schnelle und einfache Produktion in großen Mengen sowie die Inkorporationsfähigkeit großer Transgenkassetten [74]. Im Laufe der Jahre wurden verschiedene Modifikationen zur Erhöhung der Effizienz sowie Reduktion der Nebenerscheinungen vorgenommen. Man unterscheidet zwischen Vektoren der ersten und zweiten Generation, gutless und onkolytischen Vektoren. Bei adenoviralen Vektoren der ersten Generation deletierte man zunächst das essentielle Gen E1 und optional die E3-Region, wodurch das Virus seine Fähigkeit zur Replikation verlor und Transgene von bis zu 8,2 kb Größe eingebaut werden konnten [75]. Der Nachteil dieser Vektoren zeigte sich jedoch in Form von Antikörpern gegen das Virus, wodurch die Wirksamkeit in vivo limitiert war. Aus diesem Grund wurde bei Vektoren der zweiten Generation der kodierende Bereich aus den Regionen E1, E3 und E4 entfernt, wodurch zum einen die Verpackungskapazität auf 14 kb angehoben, zum anderen die adaptive Immunantwort des Wirtes gegen das Virus stark minimiert wurde [76-78]. Die Verpackung beider Generationen von Vektoren erfolgt auf speziellen, transkomplementierenden Zelllinien, die die für die Replikation essentiellen Gene zur Verfügung stellen [79]. Als weitere Modifikation wurden alle kodierende Bereiche des Virusgenoms entfernt, lediglich die Sequenzelemente für die Genomreplikation und -verpackung wurden erhalten. Die Verpackung dieser gutless-Vektoren ist nunmehr nur mit Hilfe von Helferviren möglich, die außer der E1-Region alle notwendigen regulatorischen Elemente und Struktur- Einleitung 11 gene zur Verfügung stellen [80]. Eine weitere Gruppe der adenoviralen Vektoren stellt eine Besonderheit dar, da in diesem Fall die bestmögliche Lyse von Tumorzellen im Vordergrund steht. Um dies zu erreichen, wurden bei onkolytischen Vektoren entweder essentielle Gene unter die Kontrolle von tumor- bzw. gewebespezifischen Promotoren gesetzt oder essentielle Gene deletiert, die durch einen Defekt in der Tumorzelle komplementiert werden können [81]. Adenovirale Vektoren wurden neben ihrer Anwendung in der somatischen Gentherapie auch schon als Vakzinvektoren eingesetzt (s. o.). Getestet wurden dabei unter anderem Vakzine gegen HIV, Ebola, Influenza und Tuberkulose [82-84], wobei in den meisten Fällen auf Adenovirus Typ 5 (AdV) zurückgegriffen wurde [85, 86]. Ein Problem stellt dabei jedoch die teilweise hohe Prävalenz einer anti-AdV Immunität dar, die einen negativen Einfluss auf die Induktion einer Transgenspezifischen Immunantwort haben kann [87-89]. Aufgrund eines interferierenden Präimmunstatus trat nach der zweiten Applikation desselben Viruses ein reduzierter Immuneffekt auf [90-93]. Zudem zeigte sich in der von der Firma Merck durchgeführten Step-Studie, bei der HIV-Risikogruppen dreimalig mit für HIV Nef/Gag/Pol kodierenden adenoviralen Vektoren geimpft wurden, dass eine Seropositivität für den Vektor die Infektion von Immunzellen durch HIV begünstigte [94]. Wegen dieser hohen Prävalenz treten weniger verbreitete Serotypen, wie zum Beispiel Ad11, Ad35 und Ad49, immer mehr in den Fokus [95-97]. Durch heterologe Vakzinierungen mit 2 immunologisch verschiedenen Viren oder auch durch Manipulation des Viruskapsids selbst [98] wurde dieser negative Effekt umgangen [53, 99, 100]. Dennoch zeigte sich in zahlreichen Immunisierungsstudien der positive Einfluss von adenoviralen Vektoren, die neben einer humoralen Antwort auch hohe CTL-Antworten in Form cytoxischer CD8+ T-Lymphozyten induzieren können. Aufgrund fehlender kostimulatorischer Signale oder zu geringer immunstimulatorischer Eigenschaften der meisten Proteinvakzine muss bei ihnen auf den Einsatz von Adjuvantien zurückgegriffen werden. Dies ist bei adenoviralen Vektoren nicht erforderlich, da diese als Toll-likeRezeptor-Liganden selbst kostimulatorisch wirken. Die Immunantwort gegen adenovirale Vektoren ist nicht nur gegen das übertragene Transgen, sondern auch gegen intrinsische Komponenten des Virus, nämlich die Kapsidkomponenten, gerichtet. Das Fiberprotein wirkt in vitro mitogen und induziert eine IFNγ-Expression von T-Zellen. Es ist es neben dem Hexon eines der Hauptziele von Antikörpern. Die Pentonbasis, die Mit-Initiator des Internali- Einleitung 12 sierungsprozesses ist, spielt hingegen eher eine Rolle bei der Induktion intrazellulärer Signale, bspw. in Form der Alpha-Integrin vermittelten Aktivierung des ErkSignalweges, und somit bei der Weiterleitung immunmodulatorischer Signale [101, 102]. Die initiale Immunantwort untergliedert sich in zwei Phasen. Innerhalb von 24 h nach Infektion greift die Dosis-abhängige angeborene Immunantwort, durch die etwa 80% der Viren beseitigt werden [101, 103]. In histologischen Untersuchungen nach intramuskulärer Injektion von Adenoviren fand sich eine Infiltration von Makrophagen, CD11b-positiven Neutrophilen, T-Zellen sowie natürlichen Killerzellen, welche die Viruspartikel internalisierten. Die chemische Inhibition der Ansäuerung belegte, dass vermutlich der Austritt aus dem Endosom durch Kapsidkomponenten essentiell ist, um anschließend eine Zytokin-Expression zu induzieren [104]. Außerdem wird dadurch die Möglichkeit gegeben, Fragmente von Kapsidproteinen über MHC-IKomplexe zu präsentieren [105]. Transkriptionsdefekte bzw. UV-inaktivierte Viren rufen interessanterweise ein gleiches Zytokinmuster hervor, da auch sie aus den Endosomen entlassen und über MHC-I präsentiert werden können [106]. Die durch adenovirale Vektoren induzierte Zytokinproduktion reicht von IFNγ, IFNβ, TNFα, IL-6, IL-12 über MIP-2 und RANTES [107, 108]. Zhu et al. belegten durch den Vergleich von Wildtyp- bzw. IFNα/β-Rezeptor-Knockout-Mäusen die wichtige Rolle von Typ I Interferonen bei der Beseitigung des Virus belegen. zwei Stunden nach Applikation des Virus war bei beiden Mäusestämmen noch die gleiche Kopienzahl der VirusDNA in der Leber vorhanden, drei Tage später ein wesentlich höherer Kopienanteil bei den Knockoutmäusen. Die Interferon Typ I-Produktion nach Adenovirus-Infektion war MyD88-abhängig und bei plasmazytoiden Dendritischen Zellen (CD11c+B220+) herrschte eine TLR9-Abhängigkeit vor, die es bei Makrophagen nicht gab [109]. Doch auch die adaptive Immunantwort, die nach 4-5 Tagen einsetzt, ist teilweise von der MyD88-Expression abhängig, wie eine Untersuchung mit MyD88-defizienten Mäusen zeigte. Die Adenovirus-vermittelte CD8+ T-Zellantwort war in dieser Studie signifikant schwächer im Vergleich zur Antwort in Wildtyp-Mäusen [110]. Durch die mehrere Tage andauernde Genexpression und Präsentation der endogenen Antigene über MHC-I-Komplexe werden insbesondere zytotoxische T-Zellen induziert, die über ein breites Zytokinprofil verfügen. Es werden sowohl mono- als auch polyfunktionale CD8+ Zellen nachgewiesen. Für einen langanhaltenden Schutz ist zudem die Ausbildung eines Immungedächtnisses entscheidend. Bei der gegen den viralen Einleitu ung 13 Vektor gerichtete en Antwort werden ge egen das Hexonprote H ein vor alle em IgG-Antikörper ubtyps IgG G1 induziert, gegen Fiber und Penton hingegen h e eher IgG2a a [111]. des Su Durch die d hohe Im mmunogen nität des Virus V und dem damit einhergehe e enden adju uvanten Effekt sowie die Immunantwort gege en das vo om Virus getragene g Transgen stellen V e eine gute Basis B für Vakzinieru V ngsansätze dar und die könntten sich virale Vektoren somit auch a ohne Genexpression als eine e Art Pro oteinvakzin ne eignen.. 1.4 Na anopartike el Sch hon seit den d frühen n 50er Ja ahren werrden Nano opartikel ffür diagno ostische Zwecke e, z. B. be ei Latex-Ag gglutination nstests, eingesetzt [112, 113]. Mehrere positive Aspektte, wie die e gute Sta abilität in vitro v und in n vivo, die e Reduktio on unerwü ünschter Nebene effekte sow wie die zie elgerichtete e Übertrag gung von wahlweise w medikame entösen Wirksto offen, Pepttiden, Protteinen ode er Transge enen mach hen die 10--1000 nm großen partikulären Strukkturen äuß ßerst intere essant für die d Entwiccklung inno ovativer Im mpfstoffe [114]. Hierbei H werden verscchiedene Nanopartike N el eingesettzt (Abb. 1.4). Abb. 1.4 4: Übersichtt der verschiedenen nan nopartikulärren Strukturren Dargeste ellt sind sche ematische Ab bbildungen der d im Text näher n beschrriebenen Nanopartikel. Modifiziert M nach [11 15]. ng der 198 84 erstma alig beschrriebenen ISCOMs ssteht für im mmunoDie Abkürzun erende Ko omplexe, wobei w es sich s um eine Mischu ung aus vviralen Anttigenen, stimulie Phosph holipiden, Cholestero ol und dem m Saponin QuilA auss Quillaja ssaponaria handelt [116]. Die im Durchmess D ser 40 nm m großen Partikel weisen w eine käfig-fförmige, ikosahe edrische Struktur S auf, die sich aus 12 morphologis m sch gleiche en Untereiinheiten zusamm mensetzt [117, 118]]. ISCOMss werden hauptsäch h lich von M Makrophag gen und Einleitung 14 DZ aufgenommen, wobei das Saponin QuilA, ein pflanzliches Glykosid, der entscheidenen Faktor ist, um eine TH1-Antwort anstelle von Toleranz zu induzieren [119, 120]. Aufgrund seiner immunostimulatorischen Wirkung wird es auch als Adjuvanz eingesetzt und ist als ISCOMATRIXTM kommerziell erwerblich [121]. Nanoemulsionen setzen sich aus zwei Flüssigkeiten zusammen, einer dispersen und einer flüssigen Phase, wobei auch in diesem Fall die Verkleinerung der Tropfengröße in den Nanometerbereich in einer besseren Aufnahme durch dendritische Zellen resultierte [114, 122]. Die einfache Herstellung erfolgt über eine niedrig energetische Emulsifikation bei einer konstanten Temperatur [123], über das PhasenInversions-Temperatur-Konzept [124] oder über eine Hochdruck-Homogenisation [125]. Getestet wurden bislang Nanoemulsionen als Vakzine gegen HIV, Influenza, Anthrax und Hepatitis B. Hierbei wurde nach intranasaler Applikation einer 400 nm Öl-in-Wasser-Emulsion mit dem Hepatits B-Antigen HBsAg systemisch bzw. Mukosal eine Induktion von IgG- bzw. IgA-Antikörpern nachgewiesen [126]. Auch Dendrimere wurden erstmalig 1984 beschrieben, als Tomalia et al. von der Synthese von Poly(Amidoamine)-Dendrimeren (PAMAM) berichteten [137]. Die ein bis zehn nm großen Moleküle weisen die Form einer Ellipse auf. Die grobe Unterteilung erfolgt in eine zentrale Kernregion, die stark verzweigten Seitenketten und die mit funktionellen Gruppen bedeckte Oberfläche. Die schrittweise Synthese aus einem ursprünglich einmalig verzweigten Monomer lässt sich in Bezug auf mehrere Parameter (Molekülgröße, Beschaffenheit, Dimensionen, Dichte, Polarität, Flexibilität, Löslichkeit) sehr präzise kontrollieren und auch modifizieren. Ein weiterer Vorteil, wodurch sie sich für die Medikamentenübertragung eignen, sind interne Hohlräume und offene Konformationen, in die Medikamente eingebracht werden können. Außerdem sind kovalente Bindungen auf der Oberfläche aufgrund der zahlreichen funktionellen Gruppen möglich [127, 128]. Inorganische Partikel bestehen aus Kieselgel oder Aluminium. Sie variieren in ihrer Größe, Form, Porösität und dem Kernmaterial. Dieses kann sowohl aus Metallen, Metalloxiden oder Metallsulfiden bestehen und macht die Partikel so stabil, dass sie in einem breiten Temperatur- und pH-Bereich eingesetzt werden können[129-134]. Eine besondere Form stellen die zehn nm großen Quantum Dots dar, die zwar nicht für Vakzinierungsansätze verwendet werden, aber aufgrund ihrer hohen Photostabilität und den kleinen Emissions- bzw großen Absorptionsspektren als Fluoreszenzmarker zum Einsatz kommen [135]. Einleitung 15 Nanoliposomen sind konzentrische Vesikel, die aus amphipatischen Lipidmolekülen bestehen und ein oder mehrere wässrige Kammern einschliessen [134, 136]. Ihr Einsatzgebiet erstreckt sich aufgrund der guten Biokompabilität auf kosmetische und pharmazeutische Anwendungen, aber auch im Bereich der Lebensmittelindustrie wurden Nanoliposomen bereits erfolgreich eingesetzt [137]. Bei einer Meningitis-Studie war insbesondere die Aufnahme kationischer oder Antikörperkonjugierter Nanoliposomen durch Antigen-präsentierende Zellen im Gegensatz zu früher verwendeten größeren Liposomen verbessert [46, 47]. Nanokristalle sind Aggregate von Molekülen, die in kristalline Form gebracht werden. Sie besitzen im Inneren eine hydrophobe Komponente, die von einer äußeren, hydrophilen Schicht umgeben wird. Nachteil der Nanokristalle sind die limitierte Stabilität sowie der meist aufwendige Kristallisationsprozess [134]. Zur Gruppe der auf Polymeren basierenden Partikel zählen hauptsächlich solche, die biodegradierbar sowie biokompatibel sind und sich durch eine hohe pharmakokinetische Kontrolle auszeichnen. Zu den natürliche Polymeren zählt unter anderem Chitosan, ein kationisches lineares Polysaccharid bestehend aus Glukosamin und N-Acetylglukosamin. Chitosan-Partikel werden insbesondere von Lysoyzm enzymatisch abgebaut, wobei dieser Prozess langsam erfolgt und das enthaltende Antigen über einen längeren Zeitraum ausgeschieden wird. Eine wesentliche Verlängerung des Abbauprozesses und somit der Abgabe des Wirkstoffes kann durch den Ersatz von synthetisch hergestellten Polymeren erzielt werden [138, 139]. Zu den künstlichen Polymeren zählen Polylactidsäure (PLA), Polyglycolid (PGL) sowie das am häufigsten eingesetzte Poly(lactid-co-glycolid) (PLGA). Die gute Biodegradierbarkeit beruht dabei auf der hydrolytischen Spaltung der Esterbindungen in die Originalmonomere Glykolsäure und Milchsäure. Diese Abbauprodukte liefern gleichzeitig die Erklärung für die meist mit Biodegradierbarkeit einhergehende Biokompabilität, da sie als natürlich vorkommende Nebenprodukte auch in den körpereigenen Metabolismus eingehen und über den Citratzyklus verstoffwechselt werden können [134, 140, 141]. Ein bereits kommerziell erhältliches Wirkstoffübertragungssystem mit PLGA-Partikeln ist Lupron Depot®, welches erfolgreich bei der Behandlung von fortgeschrittenem Prostatakrebs zum Einsatz kommt [142]. Bei VLPs, Virus-like-particles, handelt es sich um selbst-assemblierende Partikel bestehend aus ein oder mehreren in vitro exprimierten viralen Proteinen. Bislang sind zwei VLP-basierende Impfstoffe auf dem Markt, einer gegen Hepatitis B mit HBsAg Einleitung 16 als Antigen [119, 143] und VLPs, die aus dem großen Kapsidprotein des humanen Papillomavirus (HPV) bestehen [144]. Zur Zeit werden aber auch einige therapeutische Ansätze verfolgt, u. a. mit VLPs, die auf den RNA-Bakteriophagen Qβ basieren. Dabei wird ein Selbst-Antigen kovalent an die Oberfläche der Partikel gebunden. Dies senkte bei hypertensiven Patienten durch Induktion von Autoantikörpern erfolgreich den Blutdruck [145]. Die Virus-ähnlichen Partikel mit guten immunmodulatorischen Eigenschaften können sowohl in Hefe als auch Insekten-, Säuger- oder Pflanzenzellen produziert werden, was sie zu interessanten Vakzinekandidaten macht. Abhängig von dem eingesetzten Expressionsystem werden jedoch zu gewissen Teilen auch Proteine des Expressionssystems selbst in die VLPs eingebaut, wodurch eine Reproduktion erschwert wird. Die Immunogenität kann durch Zugabe von Kostimulantien wie z. B. Choleratoxin B [146] oder immunregulatorischen Substanzen wie z.B. GMCSF erhöht werden [147]. Polystyren-Nanopartikel weisen eine sehr variable Größe von 20 nm bis 5 µm auf und bestehen aus einem soliden Kern. Abhängig von der gewünschten Eigenschaft lassen sich verschiedene funktionelle Gruppen auf der Oberfläche anbringen, bspw. Amino- oder Carboxylgruppen. Die Partikel sind inert und neutral, dass heißt, dass auf ihnen gebundene Antigen gibt die Ladung an. Ein oft hervorgehobener Vorteil der nicht degradierbaren Partikel ist ihre Depotwirkung, da sie über einen längeren Zeitpunkt an der Injektionsstelle nachzuweisen sind und somit längere Zeit für Immunzellen zur Verfügung stehen. Mit Polystyren-Partikeln wurden viele Studien zur Abhängigkeit der Immunreaktion von der Partikelgröße durchgeführt. Dabei waren kleinere Partikel unter 40 nm nicht auf die Aufnahme von Antigen-präsentierenden Zellen angewiesen, sondern gelangten durch die Lymphbahnen zu den sekundären lymphatischen Geweben und waren dort schon vier Stunden nach Applikation nachzuweisen. Größere, über 100 nm große Partikel hingegen verblieben an der Injektionsstelle und mussten von dort aktiv von Antigen-präsentierenden Zellen zu den Lymphknoten transportiert werden [148]. Die durch Nanopartikel induzierte Immunantwort ist so variabel wie die Trägersysteme selbst. Zwar ist eher selten das Ziel, immunsupprimierende Wirkung hervorzurufen, dennoch können Nanopartikel, die selbst keine supressiven Eigenschaften besitzen, für diesen Zweck verwendet werden [149]. So wurden beispielsweise PLGA-Partikel entwickelt, in die Kollagen Typ II eingelagert war und die damit eine inflammatorische Reaktion im Mausmodell für rheumatoide Arthritis unterdrückten Einleitung 17 [150]. In den meisten Fällen wird jedoch eher eine Immunstimulation gewünscht, die oftmals auch durch eine Erhöhung der Immunogenität der sonst schwachen konjugierten Antigene, die sonst schwach sind, erreicht wird [114]. Mögliche Gründe, neben einem adjuvanten Effekt des Partikels selbst, liefern Untersuchungen zum Einfluss der Partikelgröße, -ladung und -beschaffenheit. Während negativ geladene Partikel mit einem schwachen elektrischen Potential weniger gut phagozytiert werden, ist der Anteil an aufgenommenen Partikel, die eine positive Ladung aufweisen, wesentlich höher und auf Makrophagen und Dendritische Zellen gleich verteilt [151]. Gleichzeitig beeinflusst das konjugierte Antigen die Aufnahme, wohingegen die Gesamtgröße und Ladung des Komplexes bestimmt, ob eine TH1- oder TH2-Antwort induziert wird [114]. Die Immunisierung mit Ova-beladenen Partikel erbrachte eine TH1-vermittelte Immunantwort in Form von IFNγ produzierenden CD8+ T-Zellen, wenn es sich um Partikel zwischen 20 und 67 nm handelte. Waren die Partikel jedoch 93 bis 123 nm groß, war anstelle die IFNγ Produktion eine IL-4 Produktion vorhanden und spiegelte damit die Verschiebung der Immunantwort in Richtung TH2 wieder. Die Immunisierung und anschließende Belastungsinfektion in einem RSVModell resultierte in einem geringeren Virustiter, wenn 49 nm Partikel mit einem RSV-Antigen beladen und eingesetzt wurden [152]. Dies verdeutlicht erneut das Potential, das hinter dem Einsatz von Nanopartikeln steckt, die eine gute Alternative zu bisher eingesetzten Vektoren und Ansätzen bieten. Einleitung 1.5 18 Zielsetzung Da Proteinvakzine ohne zusätzliche Applikation von Adjuvantien schwach immunogen sind, sollten im Rahmen der vorliegenden Arbeit die Immunogenität mit Ovalbumin beladener Polystyren-Nanopartikel und nicht-Antigen-exprimierender, adenoviraler Vektoren, die Ovalbumin auf der Oberfläche präsentieren, näher untersucht werden. Bei Ovalbumin handelt es sich um ein Modellantigen, dessen immundominante Epitope in C57BL/6 Mäusen gut charakterisiert sind und gegen das somit eine Reihe von Reagenzien und Modellen zur Charakterisierung der Immunantwort zur Verfügung stehen. Zunächst sollte die Beladung der Nanopartikel unterschiedlicher Größe und deren Aufnahme von Antigen-präsentierenden Dendritischen Zellen in vitro untersucht werden. Außerdem sollte in vivo durch Immunisierung von Mäusen die optimale Applikationsroute zur Induktion zellulärer und humoraler Immunantworten gegen das Antigen evaluiert werden. In einem weitern partikulären Ansatz sollten Adenoviren, die das Antigen nur auf ihrer Oberfläche präsentieren, untersucht werden, um die mögliche adjuvante Wirkung des Kapsids näher zu beleuchten. Dazu sollte der adenovirale Vektor AdVpIXOva, welcher ein Fusionsprotein aus dem adenoviralen Protein IX und Ovalbumin exprimiert, UV-inaktiviert werden. Durch die Inaktivierung wird die Genexpression jedoch verhindert und es erfolgt nur eine Präsentation des Proteins pIX-Ova auf dem viralen Partikel, wodurch dieser als Proteinvakzine fungiert. Anschließend sollten beide Ansätze in einer gemeinsamen Studie verglichen werden, wobei auf eine gleiche Proteinmenge von 50 ng Ovalbumin normalisiert werden sollte. Es sollten nach Immunisierung von Mäusen zelluläre (CD8+ T-Zellen, CD4+ TZellen) und humorale (IgG1, IgG2a) Faktoren untersucht und vergleichend analysiert werden. Diese Studie soll zeigen, ob sich die Präsentation auf viralen Partikeln oder auf Polystyren-Nanopartikeln eventuell unterschiedlich auf die Immunogenität des Antigens auswirkt und somit eine Verbesserung der Immunantwort zur Folge hat. Material und Methoden 2 19 Material und Methoden 2.1 Material 2.1.1 Geräte und Verbrauchsmaterialien 96-, 24-, 6-Loch-Platte Nunc (Wiesbaden) 96-Loch-Platte Maxisorp Nunc (Wiesbaden) 96-Loch-Platte Polysorp Nunc (Wiesbaden) Brutschrank HS12 Heraeus Instruments (Osterode) Dampfsterilisatoren H+P Labortechnik (Oberschleißheim) Durchflusszytometer FACS Calibur Becton Dickinson (Heidelberg) Elektrophoresesystem PEQLAB Biotechnologie (Erlangen) Elektroporator Gene Pulser Excell BioRad (München) Filterpapier (Falten-, Rundfilter) Schleicher & Schuell (Einbeck) Festwinkelrotor NVT100 Beckman Coulter (Krefeld) Geldokumentationskammer Biozym (Oldendorf) Konfokalmikroskop Leica DM IRE 2 (Solms) Labor-pH-Meter Greisinger electronic (Regenstauf) Lichtmikroskop CK40 Olympus (Hamburg) Luminometer Hamamatsu Photonics (Herrsching am Ammersee) Nitrozellulose Schleicher & Schuell (Einbeck) pH-Meter GHPR 1400A Greisinger electronic (Regenstauf) Photometer (Eppendorf BioPhotometer) Eppendorf (Hamburg) Pipetten Eppendorf (Hamburg) Pipettenspitzen Starlab (Ahrensburg) Pipettierhilfe Repeater Plus Hirschmann Laborgeräte (Hamburg) Peltier Thermal Cycler PTC 200 MJ Research (Ramsey, USA) Petrischalen Sarstedt (Nümbrecht) Plattenleser Anthos Labtec Instruments Siezenheim) Reaktionsgefäße Greiner (Frickenhausen) Real Time-PCR-System Lightcycler Roche Diagnostics (Mannheim) Schüttelapparat Certomat SII B. Braun Biotech International (Melsungen) (Walz- Material und Methoden 20 Schüttelwasserbad 1086 GFL (Großburgwedel) Sterilfilter Roth (Karlsruhe) Thermoschüttler Thermomixer compact Eppendorf (Hamburg) Tiefkühlschrank -86C ULT Freezer Thermo Forma (Braunschweig) Ultraschallbad MERCK eurolab (Darmstadt) Ultrazentrifugenröhrchen Beckmann Coulter (Krefeld) Vortexer K-550-GE B Ender & Hobein AG (Bruchsal) Waagen: Analysewaage SCALTEC SPB64 Scaltec (Göttingen) Präzisionswaage SCALTEC SBH31 Scaltec (Göttingen) Wasserbad E100 Lauda (Lauda-Königshofen) Whatman-Papier Schleicher & Schuell (Einbeck) Zellkulturflaschen (25 cm², 75 cm²,175 cm²) Nunc (Wiesbaden) Zellkulturflaschen (300 cm2) TPP (Trasadingen, Schweiz) Zellsiebe BD Bioscience (Heidelberg) Zentrifugen: Mikrofuge 18 Zentrifuge Beckman Coulter (Krefeld) 6-15K Laboratory Zentrifuge Sigma (Osterode am Harz) Optima L-70K Ultrazentrifuge Beckman Coulter (Krefeld) Zentrifuge 5810 Eppendorf (Hamburg) 2.1.2 Chemikalien und Lösungsmittel Alle verwendeten Chemikalien und Lösungsmittel entsprachen dem höchsten Reinheitsgrad und sind im Folgenden alphabetisch geordnet aufgeführt. Aciclovir-Ratiopharm 500 mg Ratiopharm (Ulm) ACK Lysispuffer Bio Whitaker Acrylamid Merck (Darmstadt) Agar AppliChem (Darmstadt) Agarose Invitrogen (Karlsruhe) Aluminiumsulfat-(14-18)-hydrat AppliChem (Darmstadt) Ammoniumpersulfat Roth (Karlsruhe) Ampicillin AppliChem (Darmstadt) Material und Methoden 21 Aqua bidest. Braun (Melsungen) β-Mercaptoethanol Sigma (München) Benzylguanin NEB Biosciences Borsäure J.T. Baker (Deventer, Niederlande) bovines Serum-Albumin (BSA) Applichem (Darmstadt) Bromphenolblau Sigma (München) 2-Butanol J.T. Baker (Deventer, Niederlande) 1-(3-Dimethylaminopropyl)- Applichem (Darmstadt) 3-Ethyl-Carbodiimide-hydrochlorid Carboxyfluoresceindiacetat-N- Sigma (München) succinimidylester Calciumchlorid J.T. Baker (Deventer, Niederlande) Cäsiumchlorid Applichem (Darmstadt) Chloramphenicol Applichem (Darmstadt) Chloropromazin Sigma (München) Ciprobay Bayer (Wuppertal) Coomassie Brilliant Blue Serva (Heidelberg) Cytochalasin D Sigma (München) Dimethylformamid (DMFA) Sigma (München) Dimethylsulfoxid (DMSO) AppliChem (Darmstadt) dNTP-Mix Pharmacia (Freiburg) Essigsäure J.T. Baker (Deventer, Niederlande) Ethanol J.T. Baker (Deventer, Niederlande) Ethanolamin AppliChem (Darmstadt) Ethidiumbromid 1 % (w/v) AppliChem (Darmstadt) Ethylen-Diamin-Tetraacetat VWR (Darmstadt) FACS-Flow BD Bioscience (Heidelberg) FACS-Rinse BD Bioscience (Heidelberg) FACS-Clean BD Bioscience (Heidelberg) fötales Kälberserum (FCS) Biochrom AG (Berlin) Formaldehyd J.T. Baker (Deventer, Niederlande) Formamid (deionisiert) Sigma (München) Genestein Sigma (München) Geneticindisulfat (G418) AppliChem (Darmstadt) Material und Methoden 22 Gentamycinsulfat AppliChem (Darmstadt) Glucose AppliChem (Darmstadt) Glycerin J.T. Baker (Deventer, Niederlande) Glycin Biomol (Hamburg) Hefeextrakt AppliChem (Darmstadt) Heparin Applichem (Darmstadt) 4-(2-Hydroxyethyl)-1-Piperazin- AppliChem (Darmstadt) Hexamincobaltchlorid Hydroxycoumarinsäure Sigma (München) Ethansulfonsäure Biomol (Hamburg) Hanks´ gepufferte Salzlösung (HBSS) Gibco/Invitrogen (Karlsruhe) Isofluran Baxter (Unterschleißheim) Isopropanol J.T. Baker (Deventer, Niederlande) Kaliumacetat J.T. Baker (Deventer, Niederlande) Kaliumchlorid J.T. Baker (Deventer, Niederlande) Kaliumhydrogenphosphat Riedel-de-Häen (Seelze) Kanamycinsulfat AppliChem (Darmstadt) L-Glutamin AppliChem (Darmstadt) Luminol Sigma (München) Magermilchpulver Neuform (Zarrentin) Magnesiumchlorid J.T. Baker (Deventer, Niederlande) Meerschweinchen-Komplement Sigma (München) MES AppliChem (Darmstadt) Methanol J.T. Baker (Deventer, Niederlande) Methyl-β-Cyclodextrin Sigma (München) Natriumacetat J.T. Baker (Deventer, Niederlande) Natriumazid J.T. Baker (Deventer, Niederlande) Natriumcarbonat J.T. Baker (Deventer, Niederlande) Natriumchlorid J.T. Baker (Deventer, Niederlande) Natriumhydrogencarbonat J.T. Baker (Deventer, Niederlande) Natriumdihydrogenphosphat VWR (Darmstadt) Natriumdodecylsulfat AppliChem (Darmstadt) Natriumhydroxid J.T. Baker (Deventer, Niederlande) Nickelsulfat Applichem (Darmstadt) Material und Methoden 23 Ortho-Phosphorsäure J.T. Baker (Deventer, Niederlande) Ovalbumin Sigma (München) Ovalbumin-FITC Invitrogen (Karlsruhe) Prolong Gold Antifade Reagenz Invitrogen (Karlsruhe) Proteinase K Roche (Mannheim) RNaseA AppliChem (Darmstadt) Saponin Sigma (München) Salzsäure J.T. Baker (Deventer, Niederlande) Tetracyclin Applichem (Darmstadt) N,N,N’,N’-Tetramethylethylendiamin Sigma (München) TMB+ Dako (Hamburg) Tris-(hydroxymethyl)aminomethan AppliChem (Darmstadt) Tris-(hydroxymethyl)aminomethan-HCl Biomol (Hamburg) Triton-X-100 AppliChem (Darmstadt) Trizma®Base Sigma (München) TriZol Invitrogen (Karlsruhe) Trypsin/EDTA Biochrom (Berlin) Trypton AppliChem (Darmstadt) Tween 20 AppliChem (Darmstadt) 5-Bromo-4-Chloro-3-Indolyl-β- AppliChem (Darmstadt) D-Galaktopyranosid 2.1.3 Reagenzsysteme Adenopack 20/100 Vivascience/Sartorius (Göttingen) BCA Protein Assay Kit Pierce (Schwerte) Combizyme DNA-Polymerase-Mix Invitek (Berlin) ECL Chemiglow Alpha Innotech (San Leandro, USA) Jetsorb Gel Extraction Kit Genomed (Löhne) Ni2+-NTA Protein Purification Kit Qiagen (Hilden) NucleoSpin Extract Macherey-Nagel (Düren) NucleoSpin Plasmid Macherey-Nagel (Düren) QuantiTect Probe RT-PCR Kit Qiagen (Hilden) TOPO-TA-Cloning-Kit Invitrogen (Karlsruhe) pGEM-T-Easy Vektorsystem Promega (Mannheim) Material und Methoden 24 2.1.4 Enzyme Calf Intestinal Phosphatase MBI Fermentas (St. Leon-Rot) Klenow DNA-Polymerase New England BioLabs (Frankfurt a. M.) T4 DNA-Ligase New England BioLabs (Frankfurt a. M.) Taq-Polymerase MBI Fermentas (St. Leon-Rot) Restriktionsendonukleasen New England BioLabs (Frankfurt a. M.) 2.1.5 Nährmedien Vor Gebrauch wurden sämtliche Puffer, Medien sowie Verbrauchsmaterialien bei 121°C und 202,7 kPa für 20 Min autoklaviert [153]. Hitze-empfindliche Lösungen wurden sterilfiltriert. LB-Medium 1 % (w/v) Trypton 0.5 % (w/v) Hefeextrakt 170 mM NaCl pH 7,2 -7,5 LB-Agar 1,5 % (w/v) Agar in LB-Medium SOC-Medium 2 % (w/v) Trypton 0,5 % (w/v) Hefeextrakt 10 mM NaCl 2,5 mM KCl 10 mM MgCl2 10 mM MgSO4 20 mM Glukose Selektive Agarplatten sowie Nährmedien wurden je nach Verwendungszweck mit den unten aufgeführten Selektionsmarkern versetzt. Ampicillin-Stammlsg. (1000x) 100 mg/ml Ampicillin Chloramphenicol-Stammlsg. (1000x) 68 mg/ml Chloramphenicol (in Ethanol) Kanamycin-Stammlsg. (1000x) 50 mg/ml Kanamycin Tetracyclin-Stammlsg. (300x) 6,5 mg/ml Tetracyclin (in Ethanol) Material und Methoden 25 Medien für die Herstellung chemisch kompetenter Bakterien FSB 100 mM KCl 44 mM MnCl2 10 mM CaCl2 3 mM HCoCl3 10 % (v/v) Glycerol 10 mM Kaliumacetat pH 6,4 mit 0,1 M HCl SOB 2 % (w/v) Trypton 0,5 % (w/v) Hefeextrakt 10 mM NaCl 2,5 mM KCl 10 mM MgCl2 sterilfiltiert pH 6,8-7,0 2.1.6 Puffer und Lösungen Molekularbiolgie TAE-Puffer (50x) 40 mM Trizma®Base 5 mM NaOAc 1 mM EDTA TBE-Puffer (10x) 0,89 M Trizma®Base 0,2 M Na2EDTA 0,89 M Borsäure DNA-Ladepuffer (6x) 0,25 % (w/v) Bromphenolblau 0,25 % (w/v) Xylencyanol FF 30 % (v/v) Glycerin autoklaviert Ethidiumbromid-Stammlsg. 1 % (w/v) Ethidiumbromid Resuspensionspuffer (1000ml) 50mM Tris-Base 12mM Na2EDTA H2O 100 mg RNAse pH 8,0 mit HCl Material und Methoden Lysepuffer (1000ml) 26 200mM NaOH 35mM SDS Neutralisationspuffer (1000ml) 3M Kaliumacetat 150 ml Eisessig SDS-Polyacrylamid-Gelelektrophorese und Western Blotting 10x Elektrophoresepuffer 0,25 M Trizma®Base 1,9 M Glycin 1 % (w/v) SDS Sammelgelpuffer 0,5 M Trizma®Base 10 % (w/v) SDS pH 6,8 Trenngelpuffer 2 M Trizma®Base 10 % (w/v) SDS pH 8,8 SDS-PAGE-Probenpuffer (2x) 150 mM TrisHCl 30 % (v/v) Glycerin 1,2 % (w/v) SDS 0,0018 % (w/v) Bromphenolblau 15 % (v/v) β-Mercaptoethanol Coomassie-Färbelösung 0,1 % (w/v) Coomassie Brilliant Blue 50 % (v/v) Methanol 10 % (v/v) Essigsäure Entfärber Coomassie-Färbung 10 % (v/v) Methanol 10 % (v/v) Essigsäure Kolloidale Coomassie-Färbelösung 0,02 % (w/v) Coomassie Brilliant Blue 5 % (w/v) Aluminiumsulfat-(14-18)-hydrat 10 % (v/v) Ethanol (96%) 2 % (v/v) Ortho-Phosphorsäure Entfärber kolloidale 10 % (v/v) Ethanol Coomassie-Färbung 2 % (v/v) Ortho-Phosphorsäure Transferpuffer 8 % (v/v) 10x Laufpuffer 20 % (v/v) Methanol Material und Methoden 27 PBS-T (Waschpuffer) 0,1 % (v/v) Tween 20 in PBS (1x) Blockpuffer 5 % (w/v) Magermilchpulver in PBS-T Ablösungspuffer 62,5 mM Trizma®Base 2 % (w/v) SDS 100 mM β-Mercaptoethanol pH 6,8 mit HCl Enzymgekoppelter Immunadsorptionstest (ELISA) ELISA-Beschichtungspuffer 200 mM Na2CO3 pH 9,6 ELISA-Waschpuffer 0,5 % (v/v) Tween 20 in PBS ELISA-Blockpuffer 10 % (v/v) FCS in PBS ELISA-ECL-Substrat Lösung A 0,1M TrisHCl pH 6,6 2,5 mM Luminol 30 % (v/v) H2O2 ELISA-ECL-Substrat Lösung B 6,8 mM Hyroxycoumarinsäure in DMSO ELISA-TMB+-Stopplösung 1 M H2SO4 Lösungen für die Ni2+-Protein-Aufkonzentrierung Äquilibrierungspuffer (5x) 250 mM NaH2PO4 H2O 750 mM NaCl 50 mM Imidazol pH 8,0 Lysepuffer 50 mM NaH2PO4 H2O 300 mM NaCl 10 mM Imidazol 1 % (v/v) Triton-X-100 pH 8,0 Waschpuffer 50 mM NaH2PO4 H2O 300 mM NaCl 20 mM Imidazol pH 8,0 Material und Methoden Elutionspuffer 28 50 mM NaH2PO4 H2O 300 mM NaCl 250 mM Imidazol pH 8,0 Beladungslösung 0,1 M NiSO4 Lösungen für die kovalente Kopplung an Nanopartikel Carbonatpuffer 0,1 M NaHCO3 0,1 M Na2CO3 pH 9,6 MES-Puffer 0,1 M MES pH 5,2-6,0 mit 1 N NaOH Carbodiimid-Lösung 2 % (w/v) in MES-Puffer Innerhalb von 15 Min verbrauchen Boratpuffer 0,2 M Borsäure pH 8,5 mit 1 M NaOH Lösungen und Medien für die Zellkultur Als Grundmedien für die Zellkultur wurden folgende Fertigmedien der Firma Invitrogen/Gibco (Karlsruhe) verwendet. Dulbecco´s modified Eagle´s Medium (DMEM) RPMI 1640 CD 293 Medium (serumfrei) Je nach Verwendungszweck wurden folgende Zusätze hinzugegeben: Zellkultivierung: 2-10 % (v/v) FCS Gentamycinsulfat Ciprobay DC Medium/R-10: 10 % (v/v) FCS Gentamycinsulfat 2 mM L-Glutamin Material und Methoden 29 50 µM ß-Mercaptoethanol 5 mM HEPES (nur bei R-10) PBS 130 mM NaCl 2,6 mM KCl 1 mM Na2HPO4*7 H2O 1,7 mM KH2PO4 pH 7,4 autoklaviert PBBS 1,4 mM KH2PO4 4,2 mM Na2HPO4 1,2 mM CaCl2 4,2 mM KCl 120 mM NaCl 0,9 mM MgCl2 x 6H2O 0,8 mM MgSO4 x 7 H2O 0,6 mM Glucose 0,001 % (w/v) Phenolrot pH 7,3 10x Trypsin/EDTA 0,5 % (w/v) Trypsin 0,1 % (w/v) EDTA in 10x PBS TE 1 % (v/v) 1 M Tris-HCl pH 8.0 1 mM EDTA HBS (2x) 1,4 M NaCl 250 mM HEPES 10 mM Na2HPO4 in H2O, pH 7,12; sterilfiltriert FACS-Puffer 1 % (w/v) BSA 0,02 % (w/v) Natriumazid in PBS OD-Lyse-Puffer 0,1 % (w/v) SDS 1 mM EDTA 10 mM Tris-HCL Material und Methoden 30 CFSE-Stammlösung 5 mM CFSE in DMSO Permeabilisierungspuffer 0,1 % (w/v) Saponin in FACS-Puffer Fixierlösung 3,5 % Paraformaldehyd (Konfokal- mikroskopie) bzw. 4 % Paraformaldehyd (FACS-Analyse) 2.1.7 Plasmide pAdEasy-1 Ein adenovirales Rekombinations-Plasmid; enthält das Genom des Adenovirus Typ 5 mit Deletionen der E1- und E3-Region; durch homologe Rekombination mit pShuttle können rekombinante Adenoviren erhalten werden. pCR2.1-TA TA-Klonierungsvektor; zur direkten Klonierung von PCR Produkten mit AdenosinÜberhängen (Invitrogen, Karlsruhe). pET-SnapHis-eGFP (zur Verfügung gestellt von M.Sc. B. Grewe); kodiert für ein Fusionsprotein aus Snap-Tag, His-Tag und dem offenen Leserahmen von eGFP. Es handelt sich um einen bakteriellen Expressionsvektor. pGL_Luc3 Klonierungsvektor; kodiert für den offenen Leserahmen der Firefly-Luciferase. pShuttle-CMV Klonierungsvektor für die Herstellung rekombinanter Adenoviren mit Hilfe des AdEasy-Systems; erlaubt die Klonierung eines Transgens unter CMV-PromotorKontrolle. 2.1.8 Standards Gene RulerTM 1kb Ladder Plus Fermentas (St. Leon-Rot) Prestained Precision Protein-Standard Bio-Rad (München) Material und Methoden 31 2.1.9 Peptide OT-I OVA257-264 SIINFEKL/H2-Kb OT-II OVA323-339 ISQAVHAAHAEINEAGR/H2-b OT-III OVA262-276 EKLTEWTSSNVMEER /H2-b OT-IV OVA265-280 TEWTSSNVMEERKIKV/H2-b 2.1.10 Antikörper und Tetramere α-CD4 Überstand der Hybridoma-Zelllinie 191.1 Hamster-α-CD3 BD Bioscience (Heidelberg) Hamster-α-CD28 BD Bioscience (Heidelberg) Kaninchen-α-Ova Sigma (München) Kaninchen-α-Maus Ig-HRP Dako (Hamburg) Kaninchen-α-Maus IgG1-HRP Dako (Hamburg) Kaninchen-α-Maus IgG2a-HRP Dako (Hamburg) Maus- α-Ova Sigma (München) Fluoreszenzmarkierte Antikörper: Allophycocyanin- (APC)-α-mCD4 BD Bioscience (Heidelberg) APC-α-mCD8 BD Bioscience (Heidelberg) APC-α-mB220 BD Bioscience (Heidelberg) APC-α-mCD11b BD Bioscience (Heidelberg) APC-α-mCD11c BD Bioscience (Heidelberg) APC-α-mIL2 BD Bioscience (Heidelberg) Fluoresceinisothiocyanat-(FITC)-α-mCD11c BD Bioscience (Heidelberg) FITC-α-mCD107a BD Bioscience (Heidelberg) FITC-α-mCD86 BD Bioscience (Heidelberg) FITC-α-mTNFα BD Bioscience (Heidelberg) FITC-α-rabbit Ig BD Bioscience (Heidelberg) Perinidinchlorophyllprotein-(PerCP)- α-mCD4 BD Bioscience (Heidelberg) PerCP-α-mCD8 BD Bioscience (Heidelberg) Phycoerythrin-(PE)-mIFNγ BD Bioscience (Heidelberg) PE-Cy5.5-α-mCD3 BD Bioscience (Heidelberg) Material und Methoden TRITC-α-Phalloidin 32 BD Bioscience (Heidelberg) 2.1.11 Bakterienstämme Escherichia coli BJ5183 (Stratagene) endA1 sbcBC recBC galK met thi-1 bioT hsdR (StrR) Escherichia coli DH10B (Invitrogen) F- mcrA ∆(mrr-hsdRMS-mcrBC) φ80lacZ∆M15 ∆lacX74 recA1 endA1 araD139 ∆(ara, leu)7697 galU galK λrpsL nupG Escherichia coli DH5α (NEB Biolabs) supE44 ∆lacU169 hsdR17 recA1 (Φ80lacZ∆M15) endA1 gyrA96thi-1 relA1 2.1.12 Zelllinien HEK 293A-Zellen Humane Nierenepithelzellen, die mit Adenovirus Typ 5 transformiert wurden; zur Herstellung rekombinanter Adenoviren verwendet. HEK 293T-Zellen Humane Nierenepithelzellen, die mit Adenovirus Typ 5 transformiert wurden und das große T-Antigen des SV40 (Simian Virus 40) exprimierten; zur Herstellung rekombinanter Proteine verwendet. 911-Zellen Humane Nierenepithelzellen, die mit Adenovirus Typ 5 transformiert wurden und das große T-Antigen des SV40 (Simian Virus 40) exprimierten; zur Herstellung rekombinanter Adenoviren verwendet. Material und Methoden 33 2.1.13 Polystyren Nanopartikel Alle Nanopartikel wurden von der Firma BangsLabs/Polysciences bezogen. Die Charakteristika der eingesetzten Nanopartikel sind in Tabelle 2.1 näher aufgeführt. Tab. 2.1 Verwendete Polystyren-Nanopartikel Von den unterschiedlichen Nanopartikeln, die zum Einsatz kamen, sind die wichtigsten Charakteristika wie z.B. der mittlere Durchmesser sowie die Färbung aufgeführt. Mittlerer Durchmesser [µm] Farbe Polymerbeschreibung Oberflächenladung [µeq/g] „Parking Area“ [eq.A/grp] In dieser Arbeit verwendete Bezeichnung 0,024 weiß P(S/V-COOH) 180 217,5 24P 0,057 Dragon green P(S/V-COOH) 293 56,3 57P 0,06 weiß P(S/V-COOH) 341 45,9 60P 0,093 weiß P(S/V-COOH) 209 48,3 93P 0,093 Dragon green P(S/MAA) 293 56,3 93P 0,19 Suncoast yellow PS (nicht carboxyliert) Nicht angegeben Nicht angegeben 190P 0,22 weiß P(S/V-COOH) 86 50,3 220P 0,34 weiß P(S/V-COOH) 34 81,3 340P 0,39 Dragon green P(S/V-COOH) 94,3 25,8 390P 2.1.14 Versuchstiere Es wurden weibliche Mäuse verwendet, die bei Beginn der Vakzinierungen sechs bis acht Wochen alt waren. BALB/c (H2b/b Fv1d/d Fv2s/s Rfv3s/s) Élevage Janvier (Le Genest St Isle, Frankreich) CB6F1 (H2b/b Fv1b/d Fv2r/s Rfv3r/s) Charles River WIGA GmbH (Sulzfeld) C57BL/6 (H2b/b Fv1b/b Fv2r/r Rfv3r/r) Élevage Janvier (Le Genest St Isle, Frankreich) Material und Methoden 34 2.2 Methoden 2.2.1 Molekularbiologische Arbeitsmethoden 2.2.1.1. Polymerasekettenreaktion Die PCR − Polymerase Chain Reaction − ist ein in vitro-Genkopierverfahren, bei dem durch Oligonukleotide eingegrenzte Bereiche einer DNA exponentiell amplifiziert werden [153, 154]. Die Vervielfältigung erfolgt in 20-35 zyklischen Wiederholungen, wobei jeder Zyklus in drei Schritte untergliedert ist. Die einleitende Denaturierung der DNA, bei der die Wasserstoffbrücken zwischen den DNA-Strängen gebrochen werden, findet bei 94°C statt und ermöglicht im zweiten Schritt − dem Annealing bzw. der Hybridisierung − eine Anlagerung spezifischer Oligonukleotide an die temporär vorliegenden Einzelstränge. Die optimale Annealing-Temperatur ist dabei mit der Schmelztemperatur der jeweiligen Oligonukleotide korreliert und damit abhängig von der Basensequenz [155]. Als letzter Schritt folgt die bei 72°C durchgeführte bis zu 10 minütige Elongation, bei der die partiell doppelsträngig vorliegenden DNAMatrizen durch die thermostabile Polymerase vervollständigt werden. Es wurde das Proofreading-Polymerase-Kit nach Angaben des Herstellers verwendet. Um die Kompabilität der DNA-Fragmente bei anschließenden Ligationsreaktionen zu gewährleisten, wurde das PCR-Produkt zur Entfernung überschüssiger Proofreading Polymerase über eine Säule nach Herstellerangaben aufgereinigt. Anschließend wurde das PCR-Produkt für 30 Min bei 72°C mit Taq-Polymerase und 10 mM dATP inkubiert, wobei die terminale Transferase-Aktivität der TaqPolymerase das Anfügen eines 3’Adenin-Überhanges an die DNA-Stränge ermöglicht [156, 157]. Neben der variablen Annealingtemperatur müssen auch Zyklenanzahl und -dauer sowie das Konzentrationsgleichgewicht der Reaktionskomponenten untereinander berücksichtigt werden. Insbesondere bei zu langer Dauer der Zyklen kann es zu Leseungenauigkeiten der Polymerase und somit zu Fehlamplifikationen kommen [158]. Im Allgemeinen wurde folgende Zusammensetzung des PCR-Ansatzes sowie folgendes Programm gewählt: Material und Methoden 4 μl dNTP-Mix (2,5 mM) 5 μl OptiPerform-Puffer (10x) 2 µl MgCl2 (50 mM) 10 µl Optizyme Enhancer (5x) 1 μl sense-Primer (10 μM) 1 μl antisense-Primer (10 μM) 1 μl Template-DNA 1 µl Proofreading Polymerase ad 50 μl H2O 2.2.1.2. 35 5 Min 95°C 1 Min 95°C 1 Min 60°C 1 Min 72°C 10 Min 72°C 30x Agarose-Gelektrophorese und DNA-Elution Zur Überprüfung von PCR-Produkten und Restriktionsansätzen dienten 1% Agarosegel-Elektrophoresen [159]. Durch Anlegen der Spannung wandern die durch die Phosphatreste negativ geladenen DNA-Fragmente im elektrischen Feld Richtung Anode. Die Auftrennung erfolgt dabei der Größe nach: je kleiner das Fragment ist, desto schneller und weiter wandert es durch die siebartige Struktur des Agarosegels. Das in dem Gel enthaltene Ethidiumbromid gehört zu den DNA-interkalierenden Agenzien mit der Eigenschaft der UV-Fluoreszenz. Es schiebt sich während der Elektrophorese zwischen die Basenpaare der DNA und ermöglicht somit eine Detektion der DNA unter der UV-Bank [159]. Agarose, eine Reinform des Agars, wurde dazu mit 1x TAE-Puffer gemischt und kurz aufgekocht. Anschließend wurden bei einer Temperatur von etwa 50°C 0,01 % Ethidiumbromid-Lösung hinzugegeben. Nach dem Erstarren wurde das Gel in die Gelkammer eingesetzt, und die mit 1/6 Ladepuffer versetzen Proben − bis zu 20 µl − wurden in die Taschen pipettiert. Der Lauf erfolgte bei 120-200 V, 175 mA und 30 W für 30-45 Min. Als Molekularmarker zur anschließenden Auswertung des Gels diente der Größenmarker GeneRulerTM 1kb Ladder Plus. Die Aufreinigung von DNA-Fragmenten aus dem Agarosegel erfolgte mit Hilfe des Jetsorb Gel Extraction Kits. Dabei wurde das aus dem Gel ausgeschnittene Agarosestück mit der 3fachen Menge des ersten Puffers und 10 µl Milchlösung für 15 Min bei 52°C inkubiert. Nach einem Zentrifugationsschritt bei maximaler Geschwindigkeit für eine Minute das Pellet im ersten Puffer resuspendiert. Dies wurde wiederholt und das Pellet in Puffer 2 resuspendiert. Nach einer weiteren Zentrifugation wurde das Pellet 15 Min getrocknet und anschließend in Aqua bidest bzw. TE-Puffer pH 8,0 aufgenommen werden. Nach einer 5minütigen Inkubation bei Material und Methoden 36 50°C wurde das Reaktionsgefäß noch einmal zentrifugiert und der DNA-haltige Überstand abgenommen. Bei unzureichender Menge an DNA in Lösung wurde diese einer Fällung unterzogen und in kleinerem Volumen aufgenommen. Die Zugabe von 1/10 Volumen Natriumacetat (3 M, pH 7) diente dabei der Neutralisierung negativ geladener Phosphatreste der DNA sowie der Destabilisierung der Hydrathülle; das anschließend 2,5fach zugegebene Volumen 100 % Ethanol führte zu einer Verdrängung der Hydrathülle der Nukleinsäuren in der Lösung und damit zur Ausfällung der DNA. Eine nachgeschaltete Inkubation bei -20°C verstärkte diesen Effekt [160]. Bei der anschließenden Zentrifugation für 30 Min bei 13.000 g wurde die DNA präzipitiert und dann zweimal je 5 Min mit 500 µl 70 % Ethanol gewaschen. Die DNA wurde bei geöffnetem Reaktionsgefäß bei 37°C getrocknet und in dem gewünschten Volumen A. bidest oder TE-Puffer aufgenommen [161]. 2.2.1.3. Restriktion von DNA und Ligation von DNA-Fragmenten Bei einem Verdau durch Restriktionsendonukleasen macht man sich die spaltende Eigenschaft dieser Enzyme zu Nutze. Sie schneiden DNA nach Erkennung bestimmter Basenfolgen in Fragmente, und lassen sich daher zu Klonierungszwecken einsetzen. Für einen 50 µl Restriktionsansatz wurden 5-10 µg DNA mit 5 µl des entsprechenden 10x-Puffers sowie 1 µl Restriktionsenzym versetzt und mit A. bidest auf 50 µl aufgefüllt. Der verwendete Puffer bzw. die Inkubationstemperatur wurden den Herstellerangaben entnommen. In den meisten Fällen wurde eine 1stündige Inkubation bei 37°C durchgeführt. Die Ligation erfolgte mit Hilfe des TOPO®-TA Cloning® Kits oder dem pGEM®-T Easy Vector System. Den Vektorplasmiden waren 3’-terminal Thymidine angehängt, die eine Rückkehr in den zirkulären Zustand verhindern und die Ausbeute der Ligation mit Fremd-DNA erhöhen sollten. Neben einem Ampicillinresistenzgen, welches eine Selektion über dieses Antibiotikum ermöglichte, besaß der Vektor M13, T7- sowie SP6 RNA-Polymerase Promotor-Bindungsstellen, welche bei der Überprüfung der Klonierung und den anschließenden Sequenzierungen zum Einsatz kamen. Diese flankierten die multiple Klonierungsstelle (multiple cloning site, MCS), die zudem die für das α-Peptid der ß-Galaktosidase kodierende Sequenz enthielt [162]. Bei erfolgreicher Insertion der Fremd-DNA verschiebt sich das Leseraster, so dass meistens ein inaktives Protein entsteht und eine blau-weiß-Selektion bei der Trans- Material und Methoden 37 formation möglich ist [163]. Zur Ligation wurden 5 µl DNA mit 1 µl Vektor, 1 µl T4 Ligase, 11 µl A. bidest sowie 2 µl Ligase Puffer in ein Reaktionsgefäß pipettiert und 2 h bei Raumtemperatur oder − um die Ausbeute zu erhöhen – für längere Zeit bei 16°C inkubiert. Bei schwierigen Klonierungsansätzen wurde zur Verbesserung der Ligationseffizienz vor der Elution eine Phosphorylierung bzw. Dephosphorylierung durch Zugabe von 1 µl T4-Polynukleotidkinase und 1 mM ATP bzw. 1 µl alkalische Phosphatase durchgeführt. Die Reaktion fand jeweils für 30 Min bei 37°C statt, und das Produkt wurde anschließend säulenchromatographisch aufgereinigt. 2.2.1.4. Transformation und Herstellung chemisch kompetenter Bakterien Für die Hitzeschocktransformation wurden 2 µl Ligationsansatz mit 50 µl kompetenten DH5α Zellen 30 Min auf Eis inkubiert. Zur Induktion der Plasmideinschleusung wurde das Reaktionsgefäß für 30 Sekunden in ein auf 42°C temperiertes Wasserbad gehalten, anschließend erfolgte eine weitere Inkubation auf Eis für 2 Min [164]. Nach Zugabe von 200 µl SOC-Medium wurden die Zellen für 1,5 h bei 37°C im Wärmeschrank geschüttelt. Die erfolgreiche Transformation wurde über Antibiotika-haltige Selektionsplatten überprüft, auf denen je 100 µl Transformationsansatz ausplattiert wurden. Die TA-Klonierung wurde über IPTG/X-Galhaltige Selektionsplatten überprüft. Durch die Inaktivierung des L-Peptides der ßGalaktosidase bei erfolgreicher Ligation konnte X-Gal nicht mehr gespalten werden, und rekombinante Transformanten entwickelten sich nach üN-Inkubation bei 37°C zu weißen Kolonien auf der Platte [158, 165]. Neben den von NEB Biolabs bezogenen kompetenten Zellen wurden diese auch selbst erzeugt. Für die Herstellung chemisch kompetenter Zellen wurden 5 ml LBMedium mit 2 µl transformationskompetente Zellen angeimpft und üN bei 37°C im Wärmeschrank geschüttelt [164]. Diese üN-Kultur wurde dann in 2 l SOB-Medium überführt und bis zu einer OD600=0,5±0,2 kultiviert, was der logarithmischen Wachstumsphase entsprach [165]. Anschließend wurden die Bakterien auf Eis abgekühlt und für 12 Min bei 3200 g bei 4°C zentrifugiert. Das Pellet wurde in 1/3 des Ursprungsvolumens FSB unter vorsichtigem Schwenken resuspendiert und für weitere 10 Min zentrifugiert. Die Resuspendierung erfolgte in 1/12,5 des ursprünglichen Volumens FSB unter Zugabe von 1,9 ml 3,5 % DMSO. Nach 5 Min Inkubation kamen weitere 1,9 ml 3,5 % DMSO dazu, und die Bakterien wurden für 10 Min weiter Material und Methoden 38 inkubiert. Anschließend konnte die Bakterienlösung aliquotiert, in Stickstoff schockgefroren und bis zum Gebrauch bei -80°C gelagert. 2.2.1.5. Herstellung und Transformation elektrokompetenter Bakterien Für die Herstellung elektrokompetenter Bakterien wurden 10 ml LB-Medium mit 2 µl DH10B bzw. BJ5183 Zellen angeimpft und über Nacht bei 37°C inkubiert. Der Bakterienstamm BJ5183 weist eine Streptomycin-Resistenz auf; aus diesem Grund wurden zusätzlich 30 µg/ml Streptomycin hinzugegeben. 1 ml der üN-Kultur wurde in 1 l LB-Medium verdünnt, auf 8 Zentrifugenröhrchen verteilt und für 4-5 h bis zu einer OD600=0,8 inkubiert. Nach einer Inkubation auf Eis für 1 h wurden die Zellen bei 2600 g für 10 Min bei 4°C pelletiert, in insgesamt 1 l sterilem, eiskaltem Wasser mit 10 % Glycerol resuspendiert und anschließend für 30 Min bei 2600 g abzentrifugiert. Die letzten beiden Schritte wurden ein weiteres Mal durchgeführt, wobei abschließend nicht der gesamte Überstand verworfen wurde, sondern 20 ml aufbewahrt wurden, in denen die Resuspendierung erfolgte. Nach einem letzten Zentrifugationsschritt bei 2600 g für 10 Min wurde das Zellpellet in 5 ml (bzw. 2 ml bei BJ5183) des Überstandes resuspendiert und aliquotiert. Bis zum Gebrauch lagerten die Bakterien bei -80°C. Die Transformation erfolgte in vorgekühlten 2 mm-Elektroporationsküvetten, wobei 0,1-1 µg DNA vorgelegt wurden. Nach Zugabe von 50 µl DH10B Bakterien erfolgte die Elektroporation bei einer Spannung von 2,5 kV. Anschließend wurden 200 µl SOC-Medium dazugegeben, die Bakterien für 1 h bei 37°C inkubiert und danach auf Selektionsplatten ausgestrichen. Für die homologe Rekombination zur Herstellung adenoviraler Vektoren wurde das gewünschte Transgen in das Plasmid pShuttle-CMV, welches Teile des Adenovirus-Genoms enthält, eingefügt und anschließend linearisiert. Nach einem Entsalzungsschritt wurden 5 µl Plasmid-DNA mit 50 µl Bakterien elektroporiert. Die verwendeten Bakterien sind zuvor mit dem Plasmid pAdEasy-1 vortransfomiert worden. Dieses enthält homologe Bereiche zu der Sequenz im pShuttle-CMV-Plasmid, wodurch es zu einer Rekombination zwischen beiden kommen kann und das Transgen in das adenoviralen Konstrukt transferiert wird. Die Selektion erfolgte auf Kanamycin/Ampicillin-Platten. Die anschließende Analyse der Klone wurde über einen Restriktionsverdau mit HindIII durchgeführt. Material und Methoden 2.2.1.6. 39 Identifizierung rekombinanter Klone und Plasmid-Präparation Nach der Transfomation wurden auf den Selektionsplatten gewachsene Klone mit einer Pipettenspitze gepickt und damit neue üN-Kulturen angeimpft. Die PlasmidPräparation im analytischen Maßstab (Mini-Präp) erfolgte mit Hilfe des NucleoSpin Plasmid DNA Kits nach Angaben des Herstellers, wobei das Prinzip auf einer alkalischen Lyse mit anschließender säulenchromatographischen Aufreinigung basiert. Von positiven Klonen wurden 300 ml TB-Medium mit 200 µl üN-Kultur für eine Plasmid-Präparation im präparativen Maßstab (Maxi-Präp) neu angeimpft, über Nacht bei 37°C inkubiert, für 10 Min bei 5000 g pelletiert und in 10 ml P1 resuspendiert. Die Zugabe einer Spatelspitze Lysozyms und die Inkubation für 5 Min führte insbesondere bei „low-copy“ Plasmiden zu einer erhöhten DNA-Ausbeute. Anschließend wurden 15 ml P2 Lysepuffer hinzugegeben und das Bakterienzentrifugenröhrchen sechs mal invertiert. Nach einer weiteren Inkubationszeit von 5 Min wurden 25 ml P3 Neutralisierungspuffer hinzupipettiert, 6 mal invertiert und anschließend für 10 Min bei 5000 g zentrifugiert. Der Überstand wurde durch einen Faltenfilter filtiert und mit dem 0,7 fachen Volumen Isopropanol versetzt. Nach 30minütiger Zentrifugation bei 4°C und 12000 g wurde der Überstand verworfen und das Pellet in 4,1 ml P1 mit 4,6 g Cäsiumchlorid und 40 µl Ethidiumbromid resuspendiert. Die luftblasenfrei mit der Lösung befüllten Ultrazentrifugenröhrchen wurden in den Rotor NVT100 überführt und für 4 h bei 70000 g ultrazentrifugiert. Mit Hilfe einer Spritze wird die sich farblich im Gadienten abgesetzte Bande abgenommen, mit TE-Puffer auf 4,5 ml aufgefüllt und zweimal mit 2-Butanol+10 % TE-Puffer ausgeschüttelt. Die durchsichtige, nicht mehr Ethidiumbromid enthaltende Phase wurde mit TE-Puffer auf 5 ml aufgefüllt. Nach Ethanolfällung wurde das Pellet anschließend getrocknet und üN in 500 µl TE-Puffer gelöst. Die Bestimmung des DNA-Gehaltes erfolgte über eine photometrische Messung der Absorption bei 260 nm, wobei eine optische Dichte von 1 50 µg/ml dsDNA entspricht. Material und Methoden 40 2.2.2 Proteinbiochemische Methoden 2.2.2.1. Proteinexpression Ein für die bakterielle Proteinexpression optimiertes Plasmid wurde in den IPTG-induzierbaren Bakterienstamm BL21 transformiert. Dabei handelte es sich um das Plasmid pET-SnapHis-eGFP (im Rahmen der vorliegenden Arbeit als pET-GFP bezeichnet), welches freundlicherweise von M. Sc. Bastian Grewe zur Verfügung gestellt wurde. 3 ml einer üN-Kultur wurden in 80 ml LB-Medium verdünnt und bis zu einer OD600=0,5-0,6 wachsen gelassen. Damit wurden weitere 2 l Medium angeimpft und ein weiteres Mal bis zur OD600=0,5-0,6 inkubiert. Die Induktion der Proteinexpression erfolgte durch Zugabe von 0,5 mM IPTG und einer Inkubation bei 25°C für 5 h. Anschließend wurde die Kultur abzentrifugiert, in Aliquots schockgefroren und bei -80°C gelagert. Als Vorbereitung für die Aufreinigung wurde ein Aliquot in eiskaltem PBS resuspendiert und mit 50 mg/ml Lysozym in 10 mM Tris pH 8,0 versetzt. Nach einer 3minütigen Inkubation auf Eis wurden eine Spatelspitze DNase sowie 2 % Triton-X-100 dazugegeben und unter vorsichtigem Schütteln zur Solubilisierung der Proteine weitere 30 Min inkubiert. Anschließend wurde die Lösung bei 12000 g für 30 Min zentrifugiert und der proteinhaltige Überstand abgenommen. 2.2.2.2. Proteinaufreinigung über Ni2+-NTA-Säulen Die affinitätschromatographische Aufreinigung der Fusionsproteine erfolgte mit Hilfe des Ni2+-NTA Protein Purification Kits nach Angaben des Herstellers. Die Methode basiert auf der reversiblen Bindung von Histidinen, die in den Fusionsproteinen als 6-Histidin-Tag enthalten sind, an Nickelmoleküle in der Säule. Durch Erhöhung der Imidazolkonzentration konkurriert das im Puffer enthaltene Imidazol mit den Bindungsstellen und verdrängt im letzten Aufreinigungsschritt das Protein von der Säule. 2.2.2.3. Proteinbestimmung mittels der BCA Methode 25 µl der BSA-Standardlösungen mit einer Konzentration von 0-2 µg/ml bzw. der zu bestimmenden Proteinprobe wurden mit 200 µl Arbeitslösung des BCA Protein Assay Kit für 30 Min bei 37°C inkubiert, auf RT runtergekühlt und anschließend die OD550 bestimmt. Anhand der Eichgrade der Standardlösungen wurde der Proteingehalt der Proben in µg/ml ermittelt. Material und Methoden 2.2.2.4. 41 Denaturierende Polyacrylamid-Gelelektrophorese Die Auftrennung von Proteinen aufgrund ihres Molekulargewichtes erfolgte durch eine diskontinuierliche, eindimensionale SDS-Polyacrylamid-Gelelektrophorese unter reduzierenden Bedingungen nach LAEMMLI [166]. Das Detergenz SDS verleiht den unterschiedlich geladenen Proteinen dabei eine einheitliche negative Ladung, indem es über seinen unpolaren Molekülteil mit den hydrophoben Proteinbereichen in Wechselwirkung tritt. Die Auftrennung ist somit unabhängig von der Eigenladung und abhängig vom Molekulargewicht der einzelnen Proteine. In die vertikale Elektrophoresekammer wurde das Trenngel (Tab. 2.2) kurz nach Zugabe des Polymerisationsbeschleunigers Ammoniumperoxysulfat eingefüllt. Um eine gleichmäßige Oberfläche des Trenngels und somit verbesserte Laufeigenschaften zu erreichen, wurde es mit etwas Isopropanol überschichtet. Nach der Polymerisation wurde der Alkohol vorsichtig abgeschüttet, das Trenn- mit dem Sammelgel überschichtet und ein Kamm eingeführt. Tab. 2.2: Zusammensetzung der SDS-Gele Trenngel (10 %T) Sammelgel (4 %T) Acrylamid-Bisacrylamid (30 %) 4 ml 560 µl Trenngelpuffer pH 8,8 6 ml - - 2 ml Aqua bidest 1,8 ml 1,4 ml Ammoniumperoxysulfat (25 %) 120 µl 40 µl N,N,N’,N’Tetramethylethylendiamin 10 µl 6 µl Sammelgelpuffer pH 6,8 Die Proben, von denen anschließend ein Endvolumen von 30 µl eingesetzt wurde, wurden vor dem Pipettieren in die Taschen mit SDS-Probenpuffer versetzt und 20 Min bei 95°C denaturiert. Als Größenmarker diente der Precision Plus Protein Standard. Nach Start des Gels erfolgte der Lauf bei 120 V für 2 h bis die Lauffront am unteren Ende aus dem Gel getreten war. Zum einen konnten nun die aufgetrennten Proteine auf eine Nitrozellulosemembran übertragen oder zum anderen mittels einer Coomassie-Färbung sichtbar gemacht werden. Material und Methoden 42 Für die normale bzw. die etwas sensitivere kolloidale Coomassie-Färbung wurde das Gel so lange in der Färbelösung inkubiert, bis es stark blau gefärbt war. Anschließend wurde das Gel mehrmals in Entfärber-Lösung gewaschen, bis klare Proteinbanden zu identifizieren waren. Zu Dokumentationszwecken wurde das Gel eingescannt. 2.2.2.5. Western Blot Die auf dem Acrylamid-Gel aufgetrennten Proteine wurden in einer Blotapparatur bei 100 V für 1 h auf eine Nitrozellulose-Membran transferiert. Anschließend wurden freie Bindungsstellen blockiert – und somit unspezifische Bindung verhindert – indem die Membran in Blockpuffer inkubiert wurde. Nach einem Zeitraum von 1-12 h wurde die Membran in Blockpuffer mit dem primären Antikörper überführt. Auch dieser Inkubationsschritt konnte zwischen 1 h bis 12 h variieren. Nach viermaligem Waschen mit PBS-T wurde die Membran für 1 h in Blockpuffer inkubiert, der mit HRP (horseradish-peroxidase)-gekoppeltem Sekundär-Antikörper versetzt war. Erneut folgten vier Waschschritte mit PBS-T. Die Proteinbanden wurden mit Hilfe des ECL Chemiglow-Kits detektiert, wobei die chemilumineszente Reaktion durch eine CCDKamera im Hamamatsu-Luminometer sichtbar gemacht wurde. 2.2.2.6. Kovalente Bindung von Proteinen an carboxylierte PolystyrenNanopartikel Für die Kopplung von Proteinen an die verschiedenen Nanopartikel (Tab. 2.1) wurde die gewünschte Menge an Polystyren-Nanopartikel in ein Reaktionsgefäß pipettiert und mit 500 µl 0,1 M Carbonatpuffer aufgefüllt. Da sich die kleineren 24, 57 bzw. 60 nm Partikel nicht abzentrifugieren ließen, wurden diese auf 100 kDa MWCOSäulen (Microcon) pipettiert und bei 10.000 g so lange zentrifugiert, bis die Flüssigkeit durchgelaufen war. Auf diese Weise wurde auch bei den folgenden Schritten verfahren. Partikel zwischen 61-100 nm wurden bei 20.000 g, Partikel zwischen 100250 nm bei 11.000 g und Partikel > 250 nm bei 9300 g zentrifugiert. Nach Resuspendierung der Partikel in 0,1 M Carbonatpuffer wurde dieser Schritt wiederholt, und die Partikel wurden anschließend in 750 µl MES-Puffer aufgenommen. Auch dieser Schritt wurde nach entsprechender Zentrifugation wiederholt. Nun wurden die Partikel in MES-Puffer resuspendiert, und das gleiche Volumen einer 2 % Carbodiimid-(EDAC)-Lösung wurde tropfenweise unter leichtem Schütteln hinzu- Material und Methoden 43 pipettiert. Diese wurde erst kurz zuvor hergestellt und diente der Aktivierung der Carboxylgruppen auf den Partikeln. Anschließend wurden die Reaktionsgefäße auf einem End-to-End-Mixer befestigt und 3-4 h bei RT inkubiert. Es folgte ein Waschschritt mit MES-Puffer zur Entfernung überschüssigen Carbodiimids und danach eine Resuspendierung in 0,2 M Boratpuffer. Diese Partikel wurden nun zu 50-400 µg Protein pipettiert und über Nacht bei RT auf einem End-to-End-Mixer inkubiert. Am nächsten Tag wurden die Partikel abzentrifugiert und der Überstand einer Proteinbestimmung unterzogen. Anhand der Differenz zwischen der eingesetzten und im Überstand ermittelten Proteinmenge ließ sich eine erste Schätzung der gekoppelten Menge machen. Nach zwei Waschschritten mit PBS wurden die Partikel im gewünschten Volumen PBS resuspendiert und einer Proteinquantifizierung mittels ELISA unterzogen. Die Bezeichnung der in Rahmen der Versuche eingesetzten Partikel setzt sich jeweils aus der Größe in nm sowie dem Namen des kovalent gebundenen Proteins zusammen, z.B. 93POva. 2.2.3 Zytologische Methoden 2.2.3.1. Kultivierung von Zelllinien Die Kultur der Zelllinien erfolgte abhängig von der Flaschengröße mit unterschiedlichen Volumina des entsprechenden Mediums bei 37°C, 5 % CO2 und 90 % Luftfeuchtigkeit. Die Passage der Zellen wurde je nach Zelldichte alle 2-3 Tage durchgeführt. Die adhärenten Zellen wurden zunächst mit 1x PBS gewaschen, dann kurz mit Trypsin/EDTA-Lösung inkubiert und anschließend in 5, 10 bzw. 20 ml Medium aufgenommen. Für die weitere Kultivierung wurde etwa 1/5 in einer neuen Flasche ausgesät. Für das Einfrieren von Zellen wurden diese wie oben beschrieben abgelöst und durch Zentrifugation bei 4°C, 10 Min und 1000 g pelletiert. Anschließend wurden sie in mit 10 % DMSO versetztem FCS resuspendiert und als Aliquots in flüssigem Stickstoff gelagert. Bevor die Zellen wieder in Kultur genommen wurden, mussten diese bei 37°C aufgetaut und sedimentiert werden, um das zytotoxische DMSO zu entfernen. Nun konnte die Überführung in eine 25 cm2 Zellkulturflasche erfolgen. Material und Methoden 2.2.3.2. 44 DNA-Transfektion von Zellen Insbesondere bei Transfektionen von größeren Plasmiden in eukaryotische Zelllinien wurde auf die Methode der Calcium-Phosphat-Kopräzipitation zurückgegriffen, wobei die DNA Salzkomplexe ausbildet die an die Zellmembran binden und aufgenommen werden. HEK-293T Zellen wurden am Vortag so ausgesät, dass sie 70-80 % Konfluenz aufwiesen. Zusätzlich wurde 1-2 h vor der Transfektion das Medium gegen frisches Medium ausgetauscht. 5-10 µg Plasmid-DNA sowie 31 µl 2 M CaCl2 wurden vorgelegt und mit A. bidest auf 250 µl aufgefüllt. Nach kurzem Mischen wurde dieser Ansatz langsam mit 250 µl kalter 2x HBS-Lösung unter ständigem Schwenken versetzt und für 10 Min bei RT inkubiert. Anschließend wurde der Transfektionsansatz tropfenweise zu den Zellen gegeben. Nach 5-12 h wurde das Medium erneut gewechselt. Als alternative Methode wurde die Transfektion mittels Polymeren eingesetzt, in diesem Fall Polyethylenimin (PEI). Dieses bildet zusammen mit der DNA einen Komplex, der durch Endozytose von der Zelle aufgenommen wird und mit dem Lysosom verschmilzt. Der niedrige pH-Wert innerhalb des Lysosoms führt zum Aufquellen des Polymers, der anschließenden Lyse des Lysosoms und der Freisetzung der Fremd-DNA. Für einen Ansatz in einer 25 cm2-Flasche wurden 6-8 µg PlasmidDNA mit 10 µl PEI und 500 µl serumfreien DMEM gemischt und 10 Min inkubiert. Anschließend wurde der Ansatz auf Zellen in Flaschen pipettiert, die 2 % FCS-haltiges Medium enthielten. 2.2.3.3. Expressionsanalyse von Oberflächenproteinen mittels Durchflusszytometrie Verschiedene Zellpopulationen können anhand ihrer abweichenden Größe, Granularität und dem exprimierten Proteinprofil unterschieden werden. Die Analyse erfolgt mittels Durchflusszytometrie, auch als FACS (fluorescence-activated cell sorting) bezeichnet, wobei die Proteine auf der Oberfläche mit fluoreszierenden Antikörpern markiert und anschließend im Durchflusszytometer untersucht werden. Die Zellen wurden dafür in eine 96-Rundboden-Mikrotiterplatte überführt, für 2:30 Min bei 1600 g sedimentiert, zweimal mit FACS-Puffer gewaschen und in 100 µl FACS-Puffer mit dem entsprechenden Antikörper resuspendiert, wobei die eingesetzte Verdünnung für jeden fluoreszierenden Antikörper in individuellen Titrationsexperimenten evaluiert worden war. Nach 20minütiger Inkubation bei RT im Dunkeln und Material und Methoden 45 zwei weiteren Waschschritten erfolgte die Analyse der in 200-400 µl aufgenommenen Proben nach Angaben des Herstellers an dem Durchflusszytometer FACSCaliburTM. 2.2.3.4. Virusproduktion, -anzucht, und -aufreinigung Die Produktion adenoviraler Vektoren erfolgte auf HEK-293A Zellen. Dazu wurde das Vektorgenom, das aus der homologen Rekombination hervorgegangen war, über Nacht linearisiert und am nächsten Tag in einer 25 cm2 Kulturflasche transfiziert. Nach etwa 10 Tagen ließ sich ein zytopathischer Effekt (CPE, cytopathic effect) verzeichnen, woraufhin die Zellen drei Einfrier-Auftauen-Schritten zum Zellaufschluss unterzogen wurden. Der virushaltige Überstand wurde zur Infektion weiterer Zellen und somit Anzucht des Virus verwendet, wobei die Zellzahl sukzessive erhöht wurde und so hohe Virustiter erzielt werden konnten. Vor jeder Neuinfektion wurde wieder der Aufschluss der Zellen durchgeführt. Die Aufreinigung der Viruspartikel erfolgte mit Hilfe der Kits Vivaspin Adenopack 20 bzw. 100, wobei die Partikel über Absorptionskräfte an eine Membran gebunden und so von zellulären Bestandteilen getrennt wurden. Dazu wurden Zellen in zwei bzw. fünf 300 cm2 Flaschen mit Viren infiziert und die nach Zelllyse resultierenden Überstände für die Aufreinigung nach Angaben des Herstellers verwendet. 2.2.3.5. Bestimmung der viralen und infektiösen Partikelzahl Für die Bestimmung der viralen Partikelzahl wurde der Gesamtgehalt an viraler DNA über Messung der optischen Dichte bestimmt. Nach einmaligem Einfrieren des Virusstocks wurde ein Aliquot aufgetaut, die Viren 1:10 in Lysepuffer verdünnt und 10 Min bei 56°C inkubiert. Die Messung erfolgte bei 260 nm, wobei die Bestimmung der Partikeleinheiten auf folgender Formel basiert: Virale Partikel/ml = OD260 x Verdünnungsfaktor x 1,1x1012 Die Anzahl der infektiösen Viruspartikel wurde mittels der TCID (tissue culture 50 infectious dose)-Methode bestimmt. Hier wurden HEK-293A Zellen in 96-Mikrotiterplatten ausgesäht (104 je Vertiefung) und mit seriellen, logarithmischen Verdünnungen des jeweiligen Virusstocks infiziert. Nach 6-10 Tagen wurde die infektiöse Partikelzahl bestimmt, indem für jede Verdünnung der Quotient der Vertie- Material und Methoden 46 fungen bestimmt wurde, in denen die Zellen einen zytopathischen Effekt aufwiesen. Der Wert der TCID wurde nach folgender Formel errechnet: 50 T=101+d(S-0,5) 2.2.3.6. Mit d=log10 der Verdünnungen S= Summe der Quotienten UV-Inaktivierung von Adenoviren Um den Einfluss der Transgenexpression bzw. der Proteinpräsentation auf dem adenoviralen Kapsid genauer zu untersuchen, wurde das Virus inaktiviert. Hierzu wurde der Virusstock mit bekannter Konzentration auf 1 ml aufgefüllt, mit 33 µg/µl 8Methoxypsoralen, einem Quervernetzungsreagenz, versetzt und unter UV-Licht mit einer Wellenlänge von 365 nm für 30, 60 bzw. 90 Min inkubiert [167]. Die anschließende Aufkonzentrierung über 100 kDa MWCO Micorocon-Säulen entfernte überschüssiges 8-Methoxypsoralen, welches in hohen Dosen toxisch ist [168]. Um den Einfluss der Inaktivierung auf die Transgenexpression zu überprüfen, wurden AdVGFP sowie AdVLuc, die für das jeweilige Transgen kodieren, inaktiviert. Am Tag zuvor in eine 6-Loch-Platte ausgesäte HEK-293A Zellen mit 2x109 viralen Partikeln transduziert. Nicht inaktivierte Viren dienten dabei als Positivkontrolle. Nach 72 h wurden die Zellen mittels Durchflusszytometrie bzw. luminometrischer Messung analysiert. Zudem wurde der infektiöse Titer mittels der TCID bestimmt. 50 Ob das Kapsid bzw. die Kapsid-Proteine trotz UV-Bestrahlung intakt blieben, wurde mit dem Virus AdVpIX-Ova untersucht, der freundlicherweise von Dr. Wibke Bayer zur Verfügung gestellt wurde. Dieses Virus kodiert für ein Fusionsprotein aus dem adenoviralen Kapsidprotein pIX und Ovalbumin (Ova), welches zusätzlich zur Expression in das virale Kapsid eingebaut und Ova somit auf dem Virus präsentiert wird. Im Folgenden wird das aktive, Transgen exprimierende Virus als AdVpIXOvapIX-Ova bezeichnet und das inaktivierte Virus, das nur noch das Protein auf der Oberfläche trägt, in Anlehung an die Bezeichnung der Nanopartikel als AdVpIX-Ova. Die Inaktivierung erfolgte wie oben beschrieben. Anschließend wurden HEK-293AZellen für 4 h mit 2x1010 Viruspartikel (aktiv bzw. UV-inaktiviert) inkubiert. Als Kontrollen dienten unbehandelte Zellen, Inkubation der Zellen mit 100 ng löslichem Ova sowie die Inkubation mit AdOva, einem Ova exprimierenden Vektor. Es folgte eine intrazelluläre Färbung gegen Ova und eine FACS-Analyse. War das Kapsid intakt geblieben, sollte das Virus die Zellen erfolgreich infiziert haben, und Ova in den Zellen nachgewiesen werden. Material und Methoden 2.2.3.7. 47 Generierung von myeloiden Dendritischen Zellen aus Knochenmark-Vorläuferzellen Um die Aufnahme der Nanopartikel durch Antigen-präsentierende Zellen in vitro zu bestimmen, wurden ausreichende Mengen an murinen DZ benötigt. Dazu wurden die Ober- und Unterschenkelknochen der Hinterläufe einer Maus an den Enden aufgeschnitten. Das Knochenmark wurde mit DC-Medium herausgespült. Durch mehrfachen Mediumwechsel und Zugabe der Wachstumsfaktoren rmGM-CSF (5 ng/ml) und rmIL-4 (1 ng/ml) entwickelten sich die Monozyten innerhalb von 7-10 Tagen zu unreifen murinen DZ [169]. Anschließend wurden die Zellen sedimentiert, gezählt und für nachfolgende Anwendungen eingesetzt, wobei für die FACS-Analyse immer eine Kofärbung mit einem Antikörper gegen den Oberflächenmarker CD11c erfolgte, da dieser einen spezifischen Marker für Dendritische Zellen darstellt. 2.2.3.8. Nachweis der Aufnahme von Nanopartikeln durch Dendritische Zellen Für die in vitro Aufnahme von Nanopartikeln wurden jeweils 5x105 DZ mit 50 ng löslichem Ova sowie mit 50 ng Ova beladenen Partikeln unterschiedlicher Größe für 2 h bei 4°C bzw. 37°C auf Eis bzw. im Brutschrank inkubiert. Für die durchflusszytometrische Analyse wurden die Zellen in einer Rundboden-Mikrotiterplatte abzentrifugiert, mehrmals mit FACS-Puffer gewaschen, um nicht aufgenomme Partikel zu entfernen, und mit CD11c zur Identifikation der DZ gefärbt. Da die Nanopartikel durch ein FITC-gekoppeltes Ova schon fluoreszierend markiert waren, konnte auf eine zusätzliche Färbung verzichtet werden. Anschließend wurde der Anteil an FITC-Ova-positiven Zellen bestimmt, wobei bei 4°C keine oder nur geringe Aufnahme stattfinden sollte. Für die konfokalmikroskopische Analyse wurden kommerziell erworbene, fluoreszierende Partikel verwendet. Die 57, 92 und 390 nm Partikel waren mit Dragon green, einem grün leuchtenden Fluoreszenzfarbstoff beschichtet, die 190 nm Partikel mit Suncoast yellow, einem roten Fluoreszenz-Farbstoff (Tab. 2.1). Die Zellen (5x105) wurden mit 107, 108, 109 bzw. 1010 der 390, 190, 92, bzw. 60 nm Partikel inkubiert. Anschließend wurden 105 der Zellen auf Objektträger zentrifugiert und mit 500 µl 3,5 % Paraformaldehyd für 30 Min fixiert. Nach zweimaligem Waschen für je 5 Min in PBS wurden die Zellen permeabilisiert, indem 500 µl 0,2 % Triton-X-100 in PBS auf die Zellen pipettiert wurde. Die Inkubation erfolgte für 15 Min bei RT, wobei Material und Methoden 48 sich drei Waschschritte von je 5 Min anschlossen. Nun wurden die Zellen für 30 Min bis 1 h mit 600 µl FACS-Puffer geblockt, und der Primärantikörper (α-PhalloidinTRITC bzw. α-mCD11c-FITC/APC) wurde in der entsprechenden Verdünnung auf die Zellen gegeben. Nach 1 h wurden die Zellen erneut mit PBS gewaschen und am Ende einmal kurz in A. bidest getaucht. Nachdem die Zellen getrocknet waren, wurden sie in einem Tropfen ProLong®Gold Antifade Reagent eingedeckelt, das für weitere 24 h bei 25°C aushärtete. Anschließend konnten die Proben bis zur mikroskopischen Analyse bei 4°C gelagert werden. Die Fluoreszenzaufnahmen wurden mit 63facher Vergrößerung am Konfokalmikroskop Leica DM IRE2 durchgeführt, welches Anregungen der verwendeten Farbstoffe über die Laserwellenlängen 488, 543 und 633 nm ermöglicht. Dabei wurden zur Amplifikation der spezifischen Signale gegenüber der Hintergrundfärbung jede einzelne Linie der durch die Laser abgerasterten Ebene zweimal vermessen und die Intensitäten gemittelt. 2.2.3.9. In vitro Aktivierung Dendritischer Zellen durch Antigen-beladene Nanopartikel und Adenoviren 5 5x10 Dendritische Zellen wurden für 16 h mit 10 ng löslichem Ova sowie mit 10 ng Ova beladenen Partikeln unterschiedlicher Größe inkubiert. Als Positivkontrolle dienten DZ, die mit 1 µg/ml LPS, einem nachgewiesen Aktivator der DZ, inkubiert wurden. Zudem wurden109 AdVpIX-OvapIX-Ova sowie AdVpIX-Ova eingesetzt. Die Zellen wurden nach der Inkubationszeit abzentrifugiert und der Überstand in spezifischen ELISAs auf Interferon α und β untersucht. Nach mehrmaligem Waschen der Zellen wurden diese einer α-CD11c, α-CD80 sowie α-CD86-Färbung unterzogen. CD80 und CD86 sind bekannte Aktivierungsmarker von Dendritischen Zellen, deren Expression nach der Aktivierung hochreguliert wird. Die Analyse erfolgte anschließend an einem Durchflusszytometer. 2.2.3.10. Nachweis Antigen-spezifischer T-Zell-Proliferation über einen CFSE-Verdünnnungsassay Anhand des etablierten Ovalbumin-Systems ließ sich die Proliferation von TZellen in vitro untersuchen, wobei die eingesetzten Lymphozyten aus transgenen OT-I Mäusen stammten, die nur CD8+ T-Zellen mit einem T-Zellrezeptor exprimieren, der SIINFEKL/H2-Kb Komplexe erkennt. Material und Methoden 49 Den Mäusen wurden Milz und Lymphknoten herauspräpariert und durch ein Zellsieb in Einzelzellsuspension gebracht. Die Milzzellen wurden zusätzlich einer Behandlung unterzogen, die Erythrozyten lysierte. Anschließend wurden die Zellen gewaschen und auf 1x107 Zellen/ml eingestellt. Es wurden 2 µM CFSE dazupipettiert, und die Lösung wurde unter leichtem Schütteln für 6 Min inkubiert, bis die Reaktion durch Zugabe des gleichen Volumens R10-Mediums gestoppt werden konnte. Die Zellen wurden nun mehrfach gewaschen und erneut auf eine Zelldichte von 1x107 Zellen/ml eingestellt. Die Stimulation erfolgte nach Zugabe der entsprechenden Proteine bzw. der Antigen-beladenen Dendrischen Zellen in einem Verhältnis von 1 DZ: 4 T-Zelle für 72 h bei 37°C im Brutschrank. Es wurden die gleichen Zellpräparationen wie in 2.2.3.11 beschrieben eingesetzt. Wenn sich die CFSE-markierten Zellen teilen, verlieren die Zellen die Hälfte ihre Fluoreszenzintensität und geben diese an ihre Tochterzellen weiter [170]. Diesen Prozess der Farbstoff-Verdünnung kann durch die Verschiebung in Richtung geringerer Fluoreszenzintensität bei einer FACS-Analyse beobachtet werden. Alle stimulierten Lymphozyten wurden zusätzlich mit einem gegen CD8 gerichteten, fluoreszierenden Antikörper markiert, um die Analyse auf die CD8+ T-Zellen zu beschränken. 2.2.3.11. Inhibition der Aufnahmewege von Nanopartikeln und Adenoviren durch Dendritische Zellen In einem Vorversuch wurde die maximale Dosis der Endozytose-Inhibitoren ausgetestet, indem nach der Inkubation mit unterschiedlichen Konzentrationen eine Lebendfärbung der Zellen mit anschließender FACS-Analyse durchgeführt wurde. Die getesteten Konzentrationen orientierten sich an Werten aus der Literatur [171, 172]. 106 Dendritische Zellen wurden für 1 h mit Chloropamzin (7,5 µg/ml), Methyl-βCyclodextrin (20 mM), Cytochalasin D (2 µg/ml) bzw. Genestein (200 mM) vorinkubiert. Anschließend wurden 2 µl Ova beladene Nanopartikel, 100 ng lösliches Ova sowie 2x1010 VP AdVpIX-OvapIX-Ova und AdVpIX-Ova hinzugegeben und für weitere 60 Min inkubiert. Nach dem Fixieren der Zellen wurde im Falle der mit Viren inkubierten Zellen eine intrazelluläre Färbung gegen Ova durchgeführt. Da die Partikel mit FITC-gekoppletem Ova beladen waren, konnte auf eine zusätzliche Färbung neben CD11c verzichtet werden; auch bei dem löslichen Protein handelte es sich um FITC-gekoppeltes Ova. Die Analyse erfolgte durchflusszytometrisch, wobei als Posi- Material und Methoden 50 tivkontrolle die Zellen ohne Inhibitoren, aber mit Probe inkubiert und dieser Wert auf 100 % gesetzt wurde. Die Analyse erfolgte als prozentualer Anteil der zellulären Aufnahme im Vergleich zur Positivprobe ohne Inhibition. 2.2.4 Immunologische Methoden Die Haltung der Mäuse erfolgte in der Zentralen Versuchstierhaltung der Medizinischen Fakultät der RUB nach den Richtlinien der Zentralen Versuchstierhaltung. 2.2.4.1. Immunisierung Das Immunsierungsschema für jeden einzelnen Versuch ist im jeweiligen Ergebnisteil detailiert dargestellt. Alle injizierten Lösungen wurden vorher mittels des quantitativen Detektions Kits QCL-1000® nach Herstellerangaben einem Endotoxintest unterzogen, der bestätigte, dass alle Präparationen einen Endotoxingehalt aufwiesen, der niedriger als 0,1 EU/Dosis war und somit den Richtlinien für Impfstoffe entspricht. Für den Vergleich der Immunantwort gegen lösliches Protein und Antigenbeladene Partikel wurden 6-8 Wochen alte, weibliche Mäuse des Stammes CB6F1 verwendet, der Tochtergeneration einer Kreuzung aus Balb/c und C57BL/6 (Charles River). Die 340 nm Partikel wurden mit Ova, mDec-Ova, Iso-Ova und GFP-Snap beladen und mittels eines Sandwich-ELISAs die gebundene Proteinmenge bestimmt. Es wurden zwei Mal im Abstand von zwei Wochen je 5 µg lösliches Ovalbumin bzw. auf Partikel beladen plantar verabreicht. Die Analyse der Immunantwort erfolgte 14 Tage nach der zweiten Immunisierung durch Blut- und Milzentnahme. Die Evaluierung der Immunantwort der am besten geeigneten Applikationsroute für Nanopartikel erfolgte auch mit einer Gesamtproteinmenge von 5 µg Ovalbumin, wobei dieses auf folgende Partikel geladen wurde: 24P, 60P, 93P, 220P, 340P. Die Immunsierung erfolgte entweder intramuskulär in beide M. gastrocnemii (jeweils 50 μl), subkutan (100 μl) im Bereich der Flanke, intradermal in die Plantarseite beider Hinterpfoten (jeweils 50 µl) oder intraperitoneal (100 µl). Die Analyse der Immunantwort erfolgte 14 Tage nach der Injektion durch Blut- und Milzentnahme. Für die Untersuchung der Abhängigkeit der Immunantwort von der Proteinmenge wurden 5000 ng, 500 ng bzw. 50 ng Ova auf die 93P geladen und intramuskulär in beide M. gastrocnemii (jeweils 50 μl) verabreicht. Zum Vergleich wurde Material und Methoden 51 jeweils die gleiche Menge an löslichem Ova verwendet. Die Analyse der Immunantwort erfolgte 14 Tage nach der Injektion durch Blut- und Milzentnahme. Für die vergleichende Immunatwort gegen Antigen-beladene Partikel und Adenoviren bei gleicher Proteinmenge wurden 24, 93 und 340 nm Partikel verwendet. Ein Sandwich-ELISA gegen Ovalbumin ergab, dass auf 1010 viralen Partikeln AdVpIX-OvapIX-Ova sowie dem UV-inaktivierten AdVpIX-Ova 50 ng Ova auf der Oberfläche präsentiert wurden. Die gleiche Menge wurde anschließend auch auf die Partikel beladen eingesetzt. Die zwei Immunisierungen erfolgten im Abstand von drei Wochen plantar in die Hinterpfoten weiblicher C57BL/6 Mäuse. Für die Depletion der CD4+ T-Zellen wurde am Tag -3, -1, 0, +1, +3 und +5 je 500 µl α-CD4 intraperitoneal in weibliche C57BL/6 Mäuse injiziiert. Die Immunisierung erfolgte an Tag 0, wobei in diesem Fall 500 ng Ova auf Partikeln gebunden bzw. 1010 VP verwendet wurden. Es erfolgte eine zweite Immunisierung im Abstand von drei Wochen, wobei auch hier um den Immunisierungspunkt in der vierten Woche depletiert wurde. Nach weiteren drei Wochen erfolgte die abschließende Analyse durch Milzentnahme. 2.2.4.2. In vivo Transport von Nanopartikeln Es wurden je 50 µl der 60 (1013/ml), 93 (1012/ml), 190 (1011/ml) bzw. 390 (1010/ml) nm Partikel in die Plantarseite beider Hinterpfoten appliziert. Nach 24 h wurden die poplitealen Lymphknoten entfernt und die Lymphozyten auf die gängigen Marker Antigen-präsentierender Zellen gefärbt. Dazu zählen CD11c (dendritische Zellen), CD11b (Makrophagen), B220 (B-Zellen) und CD4/CD3 (CD4+ T-Zellen). Anschließend wurde der Anteil Partikel-positiver Zellen bestimmt und zusätzlich eine Aussage über den Subtyp der Zellen gegeben. 2.2.4.3. Blutentnahme Die Tiere wurden mit Isofluran kurzzeitig narkotisiert, um retrobulbär mit einem heparinisierten Mikro-Haematokritröhrchen ca. 250 µl Blut zu entnehmen. Dieses wurde in ein Reaktionsgefäß überführt, wobei bei Plasmagewinnung Heparin hinzugefügt wurde. Anschließend wurde das Blut 10 Min bei 1000 g zentrifugiert und das Serum bzw. Plasma bis zur Antikörper-Bestimmung bei –20 °C gelagert. Material und Methoden 2.2.4.4. 52 ELISA (Enzyme linked immunosorbent assay) Zur Antikörperbestimmung aus Mausserum wurde eine Mikrotiterplatte über Nacht bei 4°C mit dem Antigen Ovalbumin (500 ng/Vertiefung) beladen. Nicht gebundenes Antigen wurden anschließend entfernt, indem die Platte 4 Mal mit ELISAWaschpuffer gewaschen wurde. Die Blockade unspezifischer Bindungsstellen auf der Platte erfolgte durch 30minütige Inkubation mit PBS+10 % FCS. Nun wurden Verdünnungen der Mausseren pipettiert, je 100 µl in jede der Plattenvertiefungen auf der Antigen-beladenen Platte, und diese für 1 h bei RT inkubiert. Nach vierfachem Waschen mit ELISA-Waschpuffer wurde der Enzym-gekoppelte Sekundärantikörper in einer 1:1000 Verdünnung in die Vertiefungen der Platte pipettiert und diese wieder für 1 h bei RT inkubiert. Nachdem auch die ungebundenen Sekundärantikörper ausgewaschen wurden, erfolgte die Detektion nach zwei unterschiedlichen Methoden. Für die Bestimmung über die optische Dichte wurden je 50 µl TMB-Substrat in die Vertiefungen der Platte pipettiert und für etwa 15 Min im Dunkeln inkubiert, wobei die Inkubationszeit bei zu geringem Farbumschlag auch erhöht werden konnte. Die Reaktion wurde durch Zugabe einer 2 N Schwefelsäure-Lösung gestoppt und die optische Dichte bei einer Wellenlänge von 450 nm bestimmt. Das Dreifache des mit naivem Serum erhaltenen Wertes wurde als Grenzwert genommen und so der Antikörper-Titer ermittelt. Die luminometrische Bestimmung des Antikörpergehalts erfolgte nach Zugabe von 50 µl einer ECL-Substratlösung, die eine im Luminometer messbare Chemilumineszenz-Reaktion in Gang setzte. Die Messgröße waren relative Lichteinheiten (RLUs) die gegen die Serumverdünnungen aufgetragen wurden. Zur Bestimmung der Proteinmenge auf den Nanopartikeln und Kapsid-modifizierten Viren wurde eine 96-Loch-Mikrotiterplatte über Nacht bei 4°C mit Maus-αOva überschichtet, wobei eine 1:1000 Verdünnung in Beladungspuffer hergestellt und je 100 µl je Loch eingesetzt wurden. Wie oben beschrieben wurde die Platte gewaschen und überschüssige Bindungsstellen wurden geblockt. Es folgte die Inkubation mit 1 µl Nanopartikeln in 99 µl Blockpuffer bzw. 5x109 viralen Partikeln (ODBestimmung) für 1 h bei RT. Nach anschließendem Waschen erfolgte zunächst die Inkubation mit einer 1:1000 Verdünnung eines Kaninchen-α-Ova-Antikörpers für 1 h. Es folgte erneutes Waschen und die Inkubation mit dem Enzym-gekoppelten Sekundärantikörpers α-Kaninchen-HRP. Die Bestimmung der Proteinmenge erfolgte über Material und Methoden 53 die luminometrische Methode, da die Nanopartikel lichtundurchlässig sind und somit die Messung über die optische Dichte nicht möglich war. 2.2.4.5. Isolierung von Lymphozyten aus der Milz Nach Tötung durch zervikale Dislokation wurde den Tieren die Milz entnommen und in HBSS überführt. Durch das Reiben der Milz durch ein Zellsieb wurden die Zellen vereinzelt, anschließend bei 1000g für 10 Min sedimentiert und für weitere 8 Min einer Erythrozytenlyse mit ACK-Lysepuffer unterzogen. Nach Stop dieser Lyse durch Zugabe gleicher Anteile HBSS wurden die Zellen erneut sedimentiert, bevor sie in R10-Medium aufgenommen und auf die gewünschte Zelldichte einstellt wurden. 2.2.4.6. Intrazelluläre Zytokinfärbung (ICS) Die zelluläre Immunantwort durch CD8+ und CD4+ T-Zellen wird über die Messung produzierter Zytokine bestimmt. Dazu werden Lymphozyten von immunisierten Tiere gewonnen und ex vivo mit spezifischem Antigen stimuliert. Anschließend werden die immunmodulatorischen Zytokine, die mit Hilfe von Monensin in der Zelle zurück gehalten werden, mit Antikörpern markiert und mittels FACS-Analyse identifiziert. Es wurden je 106 Zellen für 6 h in Gegenwart von 2 μM Monensin mit R10Medium, OT-I Peptid (2 μg/ml) zur Bestimmung der CD8+-Antwort bzw. die Mischung OT-II, IV und V (je 2 μg/ml) für CD4+-Zellen inkubiert. Zur Detektion der unspezifischen Stimulation wurden Zellen zusätzlich mit einer Kombination aus α-CD3/αCD28-Antikörpern (2 μg/ml bzw. 1 μg/ml) inkubiert. Das Gesamtvolumen der Ansätze + betrug 200 μl R10, wobei in jedem Ansatz zur Untersuchung der CD8 T-Zellen 1 μl FITC-α-CD107a Antikörper enthalten war, um die Degranulation der Zellen zu markieren. Nach sechs Stunden Inkubation erfolgte zunächst die Färbung der Oberflächenmarker mit α-CD8-PerCP oder α-CD4-PerCP Antikörper für 30 Min bei RT im Dunkeln. Nun wurden die Zellen in PBS resuspendiert und in 4 % Paraformaldehyd für 20 Min bei RT fixiert, zweimal in 200 µl FACS-Puffer gewaschen und über Nacht bei 4 °C aufbewahrt. Zur Permeabilisierung wurden die Zellen in 150 μl Permeablisierungs-Puffer aufgenommen, nach 10 Min zentrifugiert und in 100 μl αIFNγ-PE, α-IL-2-APC bzw. bei CD4+-Zellen α-TNFα-FITC Antikörper-Lösung resuspendiert. Die Antikörper wurden dazu in Permeablisierungs-Puffer verdünnt und für 30 Min zusammen mit den permeabilisierten Zellen inkubiert. Es folgten zwei Material und Methoden 54 weitere Waschschritte mit Permeablisierungs-Puffer und einer mit FACS-Puffer, bevor die Lymphozyten im Durchflusszytometer analysiert wurden. 2.2.4.7. Statistische Analyse Die statistische Auswertung wurde mittels des Programms SigmaStat durchgeführt. Nach Prüfung auf Normalverteilung wurde, soweit nicht anders angeben, eine One-Way-ANOVA durchgeführt. Abhängig von der Datenzahl wurde die Student-Newman-Keuls-Methode, Dunn’s Post hoc-Methode oder Tukey-KramerMethode angewendet. Statistische Signifikanzen (p<0,05) wurden im Text mit Stern oder Raute gekennzeichnet. Ergebnisse 3 55 Ergebnisse 3.1 Beladung von Nanopartikeln unterschiedlicher Größe durch kovalente Bindung von Protein Es sollte zunächst überprüft werden, ob die Beladung von carboxylierten Polystyren-Nanopartikeln mit aufgereinigten Proteinen durch kovalente Bindung durchgeführt werden kann und ob die Effizienz abhängig von dem verwendeten Protein variiert. Aus diesem Grund wurde ein Expressionsvektor eingesetzt, der für das Reportergen GFP kodierte. Das bakterielle Expressionskonstrukt pET-GFP (Abb. 3.1.1 A), wurde für die Produktion des GFP-Proteins verwendet und die Expression nach Transformation anhand von Fluoreszenzaufnahmen und SDS-PAGE überprüft. Schon nach Transformation des Konstruktes in kompetente Bakterien des Stammes BL21 ließ sich eine schwache GFP-Expression im Fluoreszenzmikroskop feststellen, welche nach IPTG-Induktion für 5 h stark erhöht war (Abb. 3.1.1 B-E). Zur Aufreinigung wurden die Bakterienzellen lysiert und der Protein-haltige Überstand über Ni2+-NTA-Säulen aufgereinigt. Das Protein wurde durch Imidazol-Elution von der Säule gelöst und war sowohl auf einem Coomassie-gefärbten Gel (Abb. 3.1.1. F), als auch im Western Blot detektierbar (Abb. 3.1.1. G). A T7 Prom otor His-Tag Snap-Tag HA Tag Bakterien- Durchfluss lysat #1 #2 kDa EGFP T7 Term inator B C F #1 Waschschritt #2 #3 Eluat G 230 150 100 80 60 D E 50 40 30 25 Abb. 3.1.1: Charakterisierung des exprimierten Proteins GFP Das zur Verfügung gestellte Konstrukt kodiert für den offenen Leserahmen eines Fusionsproteins aus His-Tag, Snap-Tag, HA-Tag und eGFP. Es wird flankiert von einem T7-Promotor am N-terminalen, sowie einer T7 Terminatorsequenz am C-terminalen Ende (A). Schon vor IPTG-Induktion war eine geringe Basisproduktion feststellbar (B Fluoreszenz, D Durchlicht), die durch Zugabe von 0,5 mM IPTG für 5 h stark erhöht wurde (C Fluoreszenz, E Durchlicht) Alle 4 Bilder wurden bei 200facher Ergebnisse 56 Vergrößerung aufgenommen. Von jedem Schritt der Proteinaufreinigung über Ni2+-NTA-Säulen wurden 20 µl auf ein 10 % SDS-PAGE-Gel aufgetragen und anschließend einer Coomassie-Färbung unterzogen (F). Zudem wurde vom Eluat ein Western Blot angefertigt, bei dem ein HRP-gekoppelter α-GFP-Antikörper zum Einsatz kam (G). Die FACS-Analyse der GFP-beladenen Partikel zeigte nach Inkubation mit dem Protein eine Verschiebung der Histogrammkurve in Richtung höherer Fluoreszenzintensität, d.h. die beladenen Partikel fluoreszierten stärker als unbeladene Partikel. Mit einer mittleren Fluoreszenzintensität (MFI) von 2197,5 wurde die beste Beladung bei 60 nm Partikeln nachgewiesen. Der niedrigste Wert wurde bei 340PGFP mit einer MFI von 30,2 ermittelt (Abb. 3.1.2). 24GFP Anzahl Partikel 40 194,9± 14,7 30 60GFP 75 2197,5± 51 56 93GFP 75 73,9± 9,9 56 220GFP 75 38,2± 1,3 56 38 38 38 23 10 19 19 19 11 0 0 0 0 0 1 10 2 10 3 10 4 10 0 10 1 10 2 10 3 10 4 10 0 10 1 10 2 10 3 10 4 10 30,2± 0,3 34 20 10 340GFP 45 0 0 10 1 10 2 10 3 10 4 10 0 10 1 10 2 10 3 10 4 10 GFP Abb. 3.1.2: Beladungseffizienz von Partikeln unterschiedlicher Größen mit GFP 108 der jeweiligen Partikel wurden mit 2 % Carbodiimid-Lösung in 0,1 M MES-Puffer für 3-4 h bei 37°C vorinkubiert und nach Überführung in 0,2 M Boratpuffer je 50 µg GFP hinzugefügt. Die beladenen Partikel (schwarze Kurve) wiesen eine Verschiebung der Histogrammkurve in Richtung höherer Fluoreszenzintensität auf. Als Negativkontrolle dienten unbeladene Partikel (grau ausgefüllte Flächen). Es wurden drei Messungen durchgeführt, wobei die Histogramme repräsentativ sind. Bei den angegebenen Werten handelt es sich um Mittelwerte der mittleren Fluoreszenzintensität und deren Standardabweichung. Um Unterschiede in der Kopplung abhängig vom verwendeten Protein zu untersuchen, wurden die Partikel verschiedener Größen mit einem kommerziell erworbenen, FITC-gekoppelten Ovalbumin inkubiert und anschließend einer FACSAnalyse unterzogen. Auch in diesem Fall kam es zu einer Verschiebung in der Histogrammkurve, wobei die mittlere Fluoreszenzintensität zwischen 44,8 und 359,3 schwankte. Es wurde bei den 60 nm Partikeln die beste Beladungseffizienz nachgewiesen, wobei in diesem Fall die 220 nm Partikel wesentlich besser beladen werden konnten als mit GFP-Protein (Abb. 3.1.3). Auch die Beladung von Nanopartikeln mit aufgreinigtem Luciferase-Protein resultierte in einer erfolgreiche Kopplung (Daten nicht gezeigt). Ergebnisse 24Ova 2500 Anzahl Partikel 57 134,9± 0,01 1875 60Ova 500 359,3± 0,8 375 93Ova 500 188,5± 28,3 375 220Ova 500 81,33± 1,8 375 250 250 250 250 625 125 125 125 125 0 0 0 0 0 1 10 2 10 3 10 4 10 0 10 1 10 2 10 3 10 4 10 0 10 1 10 10 2 3 10 4 10 44,8± 0,7 375 1250 10 340Ova 500 0 0 10 1 10 2 10 3 4 10 10 0 10 1 10 2 10 3 10 4 10 FITC Abb. 3.1.3 Beladungseffizienz von Partikeln unterschiedlicher Größen mit FITC-gekoppeltem Ovalbumin 108 der jeweiligen Partikel wurden mit 2 % Carbodiimid-Lösung in 0,1 M MES-Puffer für 3-4 h bei 37°C vorinkubiert und nach Überführung in 0,2 M Boratpuffer je 50 µg Ova hinzugefügt. Die beladenen Partikel (schwarze Kurve) wiesen eine Verschiebung der Histogrammkurve in Richtung höherer Fluoreszenzintensität auf. Als Negativkontrolle dienten unbeladene Partikel (grau ausgefüllte Flächen). Es wurden drei Messungen durchgeführt, wobei die Histogramme repräsentativ sind und die Werte der mittleren Fluoreszenzintensität und deren Standardabweichung dargestellt sind. 3.2 Aufnahme von Nanopartikeln durch Dendritische Zellen in vitro Als nächstes sollte untersucht erden, ob unreife Dendritische Zellen die Proteinbeladenen Nanopartikel aufnehmen. Hierzu wurden die Zellen für 30 Min bei 4°C als Negativkontrolle bzw. bei 37°C mit FITC-gekoppeltem Ova oder FITC-Ovabeladenen Partikeln inkubiert. Nach anschließendem Waschen folgten die Antikörper-vermittelte Färbung des CD11c-Rezeptors und eine durchfluss- zytometrische Analyse. Die bei 37°C inkubierten Zellen nahmen in allen Fällen einen signifikant höheren Prozentsatz an Protein bzw. Nanopartikeln auf (Abb. 3.2.1). Während bei 4°C nur 0,55 % der mit löslichem FITC-Ova inkubierten Zellen dieses aufnahmen, waren es bei 37°C 4 % (p<0,05; Dunn’s post-hoc Methode). Bei Zellen, die mit 340POva inkubiert wurden, fanden sich sogar 6,5 % positive Zellen. Ergebnisse 58 * % Ovalbumin+ Zellen 8 * * * * * * 6 4°C 37°C 4 2 va O 34 0P va O 22 0P va O 93 P va O 60 P va O 24 P lö s lic he s D O C s va 0 Abb. 3.2.1: Größenabhängige Aufnahme von Nanopartikeln durch Dendritische Zellen in vitro 5x105 unreife Dendritische Zellen wurden mit löslichem Ova bzw. den Ova-beladenenen Partikel inkubiert, wobei immer 50 ng Ova eingesetzt wurden. Die Inkubation erfolgte bei 4°C bzw 37°C. Anschließend folgte eine α-CD11c Färbung und nach mehrmaligem Waschen die FACS-Analyse. Dargestellt ist der prozentuale Anteil an FITC-Ova positiven Zellen. Die statistische Analyse ergab signifikante Unterschiede mit *= p<0,05 (Dunn’s post-hoc Methode). Zusätzlich wurden Fluoreszenzbilder mittels Konfokalmikroskopie aufgenommen. Dafür wurden fluoreszierende Partikel unterschiedlicher Größe verwendet. Aus Knochenmark gewonnene Dendritische Zellen wurden mit 57, 92, 390 bzw. 190 nm großen Partikeln inkubiert, die damit eine vergleichbare Größe zu den Protein-beladenen Partikeln aufwiesen. Die kleinsten Partikel lagen jedoch unterhalb der Auflösungsgrenze. Im Falle der anderen drei Partikelgrößen wurde die Aufnahme der Partikel einwandfrei festgestellt (Abb. 3.2.2, Abb. 3.2.3), wobei qualitativ ein Großteil der Zellpopulation die Partikel aufnahm. In den meisten Fällen kam es zu einer Anreicherung mehrerer Partikel pro Zelle (Abb. 3.2.2 oben) in Einzelfällen zu einem Transport in den Nukleus, was sich bei einer gleichzeitigen Anfärbung von DNA und somit des Zellkerns zeigte (Abb. 3.2.3). Ergebnisse 59 Partikel Dragon Green Phalloidin TRITC Überlagerung 93P 10 µm 390P 10 µm Abb. 3.2.2: Konfokalmikroskopische Analyse der Aufnahme grün fluoreszierender 92 bzw. 390 nm Partikel durch Dendritische Zellen in vitro In vitro kultivierte Dendritische Zellen (5x105) wurden für 2 h mit 107 (390 nm) bzw. 109 (93 nm) grün fluoreszierenden Partikeln inkubiert. Nach zweimaligem Waschen wurden je 105 der Zellen auf Objektträger zentrifugiert, mit 3,5 % Paraformaldehyd fixiert und das Zytoskelett anschließend mit Aktin-TRITC (rote Färbung) gefärbt. Nach dem Eindeckeln der Zellen wurden diese mittels eines Leica DM IRE 2 Konfokalmikroskops untersucht. Es wurde das Objektiv mit der 63fachen Vergrößerung verwendet. Der weiße Balken spiegelt eine Größe von 10 µm wieder. Aufgrund von Fluoreszenzfarbstoff-Limitierung konnte nur für die 190 nm Partikel sowohl DNA als auch der spezifische Dendritische Zellmarker CD11c gefärbt werden; bei den 92 nm bzw. 390 nm Partikeln musste auf eine Aktin-Zytoskelett-Färbung zurückgegriffen werden. Ergebnisse CD11c FITC 60 Partikel Suncoast Yellow DNA ToPro3 Überlagerung 10 µm Abb. 3.2.3: Konfokalmikroskopische Analyse der Aufnahme rot fluoreszierender 190 nm Partikel durch Dendritische Zellen in vitro In vitro kultivierte Dendritische Zellen (5x105) wurden für 2 h mit 108 190 nm großen, rot fluoreszierenden Partikeln inkubiert. Nach zweimaligem Waschen wurden je 105 der Zellen auf Objektträger zentrifugiert, mit 3,5 % Paraformaldehyd fixiert und die Zellen mit CD11c-FITC (grün) sowie ToPro3 (Zellkernfärbung, blau) gefärbt. Nach dem Eindeckeln der Zellen wurden diese mittels eines Leica DM IRE 2 Konfokalmirkoskops untersucht. Es wurde das Objekt mit 63facher Vergrößerung verwendet. Der weiße Balken spiegelt eine Größe von 10 µm wieder. 3.3 In vivo Transport von Nanopartikeln durch verschiedene Zell-Subtypen Der Transport von Nanopartikeln zu dem nächstgelegenen lymphatischen Gewebe ist ein wichtiges Kriterium für die Induktion einer nachfolgenen Immunantwort. Um den in vivo-Transport von Nanopartikeln zu den nächstgelegenen Lymphknoten nachzuweisen, wurden fluoreszierende Partikel plantar in die Hinterpfoten von C57BL/6 Mäusen injiziert und nach 24 h die poplietalen Lymphknoten herauspräpariert. Zudem sollte untersucht werden, welche Zellpopulation welche Größe präferentiell aufnimmt. Aus diesem Grund folgte eine Antikörper-Färbung gegen die gängigen Zellmarker von Dendritischen Zellen (CD11c), B-Zellen (B220), Makrophagen (CD11b) und CD4+ T-Zellen (CD4 und CD3). Die Analyse ergab bei allen Größen der Partikel positive Zellen innerhalb des Lymphknotens (Abb 3.3.1). Die meisten Zellen, die 57 nm Partikel internalisiert hatten, zählten zur Subpopulation der B-Zellen (B220+). Auch bei den 93 nm sowie 190 nm konnten die meisten B220+–Zellen identifiziert werden, die Partikel aufgenommen haben, wobei die Anzahl an positiven Zellen generell höher war als bei den kleineren Partikeln und auch der Anteil an Makrophagen (CD11b+) höher war. Bei den 390 nm Partikeln fanden sich insgesamt nur wenige positive Zellen, wobei in diesem Fall die Partikel von Makrophagen, B-Zellen und CD4+ T-Zellen zu gleichen Teilen aufgenommen wurden. Dendritische Zellen spielten bei allen Partikelgrößen nur eine untergeordnete Rolle. Ergebnisse A 61 B C D Abb. 3.3.1: FACS-Analyse der Lymphozyten von Partikel-immunisierten C57BL/6 Mäuse 6 bis 8 Wochen alte C5BL/6 Mäusen wurden je 50 µl der 57P (1013/ml; A), 93P (1012/ml; B), 190P (1011/ml; C) bzw. 390P (1010/ml; D) in die Plantarseite beider Hinterpfoten appliziert. Nach 24 h wurden die poplietalen Lymphknoten präpariert, die Lymphozyten isoliert und die Zellen mit den Oberflächenmarkern CD11c+ (Dendritische Zellen), CD11b+ (Makrophagen), B220+ (B-Zellen) und CD4+CD3+ (CD4+ T-Zellen) gefärbt. Anschließend erfolgte die Analyse mittels Durchflusszytometrie, wobei die Anzahl Partikel-positiver Zellen pro 106 Lymphozyten ermittelt wurde. N=3. 3.4 Transgenexpression und Infektiösität von Adenoviren nach UV-Behandlung In einem weiteren Ansatz zur Verbesserung von Protein-basierenden Vakzinen sollten UV-inaktivierte Adenoviren untersucht werden. Um die Transgenexpression nach UV-Inaktivierung zu überprüfen, wurden 2x109 virale Partikel der für GFP bzw. Luciferase kodierenden Viren AdVGFP bzw. AdVLuc für 30, 60 bzw 90 Min bei 365 nm unter Zugabe von 8-Methoxypsoralen inaktiviert. Anschließend wurde überschüssiges Psoralen entfernt und eine Infektion von HEK-293A Zellen durchgeführt. Die FACS-Analyse nach 72 h ergab bei unbehandelten Zellen einen Hintergrundwert von 0,1 % fluoreszierenden Zellen (Abb. 3.4.1). Wurden die Zellen jedoch mit aktivem AdVGFP inkubiert, kam es zu einer signifikanten Verschiebung der Fluo- Ergebnisse 62 reszenzintensität; in diesem Fall waren 92,8 % der Zellen GFP-positiv (p<0,05; Student-Newman-Keuls-Methode). Nach 30 Min UV-Inaktivierung waren noch 3,1 % der Zellen GFP-positiv, was jedoch schon eine signifikante Reduktion im Vergleich zum aktiven Virus darstellte (p<0,05; Student-Newman-Keuls-Methode). Nach 60 Min UV-Inaktivierung konnte eine weitere Reduktion der Transgenexpression festgestellt werden, nur 0,4 % der Zellen fluoreszierten. A 10 2 10 3 4 10 88 365 nm 90 Min 79 82 3,1± 0,4 % 66 0,4± 0,09 % 62 41 40 22 21 20 0 0 0 10 10 1 2 10 3 10 4 10 0 0 0 10 1 10 10 2 α-GFP 10 3 4 10 20 0,1± 0,06 % 59 44 40 0 10 10 1 2 10 3 10 4 10 in 1 10 365 nm 60 Min 90 M 0 10 in 4 10 60 M 3 10 36 5n m 2 10 in 1 30 M 10 365 nm 30 Min lle 0 10 60 36 5n m 0 FP 20 0 # 80 36 5n m 13 # * * A dV G 40 # on tr o Anzahl der Zellen 26 100 92,8± 0,2 % 60 K 0,1± 0,02 % 39 B 2x109 AdVGFP 80 % GFP+ Zellen Kontrolle 52 Abb. 3.4.1: Einfluss der AdVGFP UV-Inaktivierung auf die Transgenexpression 72 h nach Infektion Je 2x109 virale Partikel AdVGFP wurden mit 8-Methoxysporalen versetzt und für 30, 60 bzw. 90 Min unter einer UV-Lampe bei 365 nm inaktiviert. Nach Entfernung des überschüssigen 8-Methoxypsoralens wurden je 106 HEK-293A Zellen mit den Virusproben für 72 h inkubiert, wobei 108 aktive Partikel als Positivkontrolle dienten. Die anschließende Analyse erfolgte mittels Durchflusszytometrie, wobei der prozentuale Anteil an GFP-exprimierenden Zellen im Vergleich zu untransduzierten bzw. mit aktivem Virus tranduzierten Zellen ermittelt wurde. Beispielhafte Darstellung einer von drei unabhängigen Versuchsreihen (A). Zusammenfassung (B) mit *= p<0,05 zur Kontrolle und #= p<0,05 AdVGFP (Student-Newman-Keuls-Methode). Auf die gleiche Weise wurde das Virus AdVLuc inaktiviert und gleichermaßen mit HEK-293A Zellen inkubiert. Die luminometrische Messung ergab nach Zelllyse eine signifikant höhere Luciferase-Aktivität gegenüber allen anderen Proben, wenn es sich bei dem eingesetzten Virus um den noch exprimierenden Vektor handelte (p<0,05, Student-Newman-Keuls-Methode). Nach nur 30 Min Inaktivierung ließen sich noch 104 relative Lichteinheiten messen; nach 90 Min hingegen glich der Wert dem der als Negativkontrolle eingesetzten untransduzierten Zellen (Abb. 3.4.2). Parallel wurde mit allen UV-behandelten Viren eine Messung der TCID50 vorgenommen, um den infektiösen Titer zu bestimmen. Bei allen eingesetzten Viren kam Ergebnisse 63 es zu einer Reduktion um 4-5 Log-Stufen, was einer infektiösen Partikelzahl von >103/ml entsprach. RLUs [log10] 1.0×10 8 # # * * # 1.0×10 6 1.0×10 4 1.0×10 2 in 90 M 36 5n m 60 M in in 36 5n m 30 M 36 5n m dV .L uc A K on tr ol le 1.0×10 0 Abb. 3.4.2: Einfluss der AdVLuc UV-Inaktivierung auf die Transgenexpression 72 h nach Infektion Je 2x109 virale Partikel AdV.Luc wurden mit 8-Methoxysporalen versetzt und für 30, 60 bzw. 90 Min unter einer UV-Lampe bei 365 nm inaktiviert. Nach Entfernung des überschüssigen 8-Methoxypsoralens wurden je 106 HEK-293A Zellen mit den Virusproben für 72 h inkubiert, wobei 108 aktive Partikel als Positivkontrolle dienten. Es wurden die relativen Lichteinheiten nach Luciferin-Zugabe in einem Luminometer gemessen. Es wurden 3 unabhängige Experimente durchgeführt. Statistische Signifikanzen sind mit *= p<0,05 zur Kontrolle und #= p<0,05 zu Ad.Luc Kontrolle gekennzeichnet (StudentNewman-Keuls-Methode). Die Überprüfung einer möglichen Beschädigung des Kapsids durch die UV-Bestrahlung sowie die Transduktionsfähigkeit von Zellen durch das inaktivierte Virus wurde mit AdVpIX-OvapIX-Ova durchgeführt. Dieses Virus exprimiert ein Fusionsprotein aus dem adenoviralen Kapsidprotein pIX und Ovalbumin. Dieses Protein wird dadurch zusätzlich in das Kapsid eingebaut und führt zu einer Ovalbuminpräsentation auf der Oberfläche des viralen Partikels. Das inaktivierte, nicht mehr transgenexprimierende Virus wird im Folgenden als AdVpIX-Ova bezeichnet. Zunächst wurden 2x1010 aufgereinigte AdVpIX-Ova über ein SDS-Gel aufgetrennt und ein Western Blot gegen Ova durchgeführt. Die prominenteste Bande lag bei etwa 55 kDa, der Größe des Fusionsproteins pIX-Ova (Abb. 3.4.3 A). Zusätzlich wurde überprüft, ob die Ergebnisse 64 immundominanten Epitope des Virus trotz der hohen UV-Bestrahlung intakt blieben. Dafür wurden Dot Blots mit aktivem und UV-inaktiviertem Virus durchgeführt. Es wurde der in den Tierversuchen eingesetzte Virus verwendet, aber auch ein für die nachfolgenden Versuche nicht erheblicher Virus, um zu belegen, dass die Reaktion unabhängig vom eingesetzten Virus war. Die Inkubation mit Serum von Tieren, die mit Adenoviren (AdVEnv) immunisiert wurden, ergab positive Ergebnisse im Dot Blot. Die Intensität der Reaktion war dabei bei allen eingesetzten Viren, unabhängig von einer UV-Behandlung, gleich (Abb. 3.4.3 B). Um die Spezifizität des Versuchs zu kontrollieren wurde eine Probe zusätzlich mit naivem Serum behandelt. (Abb. 3.4.3 C). B A C AdVcore 75kDa 50kDa AdVcore UV-inaktiviert AdVcore pIX-Ova AdVpIX-OvapIX-Ova 37kDa AdVpIX-Ova Abb. 3.4.3: Analyse aufgereinigter und UV-inaktivierter Viruspartikel 2x1010 AdVpIX-OvapIX-Ova wurden UV-inaktiviert und über 10 % SDS-PAGE aufgetrennt. Anschließend wurden die Proteine auf eine Nitrozellulosemembran transferiert und eine Antikörperfärbung gegen Ova vorgenommen. Bei der prominenteste Bande bei etwa 55 kDa handelt es sich um das Fusionsprotein pIX-Ova, welches auf der Oberfläche der Viruspartikel präsentiert wird (A). 2x1010 virale Partikel AdVcore, einem für die weiteren Versuche nicht erheblichen Virus, und AdVpIX-OvapIX-Ova wurden UV-inaktiviert und mit der gleichen Anzahl viraler Partikel auf eine präaktivierte Nitrozellulosemebran pipettiert. Nach dem Blocken wurde die Membran mit Serum Adenovirus-immunisierter Tiere (1:1000 Verdünnung) inkubiert und anschließend mit α-Maus-HRP behandelt (B). Zur Kontrolle der Spezifizität wurde eine Probe mit Serum einer naiven Maus inkubiert (C). Für die Überprüfung der Internalisierung wurden HEK-293A Zellen mit 2x1010 viralen Partikel des inaktivierten Virus (AdVpIX-Ova) bzw. einer äquivalenten Menge an aktivem Virus (AdVpIX-OvapIX-Ova) sowie 100 ng löslichem Ova und einem Ovaexprimierenden Vektor (AdVOva, Negativkontrolle) für 4 h inkubiert und eine intrazelluläre Färbung gegen Ova durchgeführt. Während lösliches Ova nur in geringer Menge durch die nicht-phagozytierenden Zellen aufgenommen wurde, kam es nach Inkubation mit dem inaktivierten Virus bzw. dem pIX-Ova exprimierenden Virus zu Ergebnisse 65 einer Erhöhung des prozentualen Anteils an Ovalbumin-positiven Zellen (Abb. 3.4.4). Der Anteil war dabei zwischen AdVpIX-Ova und AdVpIX-OvapIX-Ova nicht unterschiedlich, was für ein Intaktbleiben des viralen Partikel sprach. AdVOva diente als Negativkontrolle, da es sich um einen Ova-exprimierenden Vektor handelt und nach 4stündiger Inkubation keine Ovalbumin detektiert wurden. % Ovalbumin+ Zellen 15 * * n. s. 10 5 A dV O va va dV A va A dV p IX -O pI XO va pI XO va O es lic h lö s K on tr ol le 0 Abb. 3.4.4: Einfluss der Inaktivierung auf die Infektiösität 2x1010 virale Partikel AdVpIX-Ova bzw. 100 ng lösliches Ova wurden für 4 h mit 5x105 HEK-293A Zellen inkubiert, diese anschließend gewaschen, fixiert und permeabilisiert, um mit Antikörpern Ova intrazellulär anzufärben. Die Analyse erfolgte durchflusszytometrisch. *=p<0,05 gegen lösliches Ova (Student Newman-Keuls-Methode). N=3 3.5 Ergebnisse zur Aktivierung von Dendritischen Zellen durch die Aufnahme von Ova-beladenen Nanopartikeln, AdVpIX-OvapIX-Ova und UV-inaktiviertem AdVpIX-Ova Um die Immunogenität Protein-beladener Partikel zu bestimmen, wurden Partikel unterschiedlicher Größe zunächst mit Ovalbumin beladen. Die Analyse der Beladung der für die Tierversuche einzusetzenden Nanopartikel sowie der Viren erfolgte anschließend zum einen qualitativ über einen Dot Blot mittels Detektion des Ovalbumins, zum anderen über einen Ova-Sandwich-ELISA, bei dem der Ovalbumingehalt auf den Partikeln quantifiziert wurde. Hierbei wurden auf 1010 viralen Partikeln ungefähr 50 ng Ovalbumin präsentiert. Anhand dieser Ergebnisse wurden die Partikelpräparationen normalisiert. Mittels eines Dot Blot, für den je Probe 100 ng Ova bzw. 2x1010 aufgereinigte virale Partikel eingesetzt wurden, ließ sich bei allen Ergebnisse 66 Proben erfolgreich Ovalbumin in gleichen Mengen nachweisen (Abb. 3.5.1). Als Negativkontrollen dienten zum einen je 2 µl unbeladene Partikel, zum anderen eine äquivalente Menge eines Ova-exprimierenden Virus (AdVOva), bei dem kein Ova in der aufgereinigten Viruspräparation nachzuweisen war. 24POva 57POva 93POva 220POva 340POva 24P 57P 93P 220P 340P lösliches AdVpIX-Ova AdVOva Ova Abb. 3.5.1: Dot Blot der mit Ovalbumin beladenen Nanopartikel, AdVpIX-Ova und entsprechenden Negativkontrollen Die Nitrozellulosemembran wurde für 5 Min in Transferpuffer präaktiviert und von jeder Partikelpräparation bzw. löslichem Protein wurden 100 ng aufgetragen und von den unbeladenen Partikeln je 2 µl verwendet. Sowohl vom UV-inaktivierten AdVpIX-Ova als auch dem AdVOva wurden 2x1010 virale Partikel eingesetzt. Nachdem die Lösung eingezogen war, wurde die Membran für 5 Min in PBS-T gewaschen und dann für 1 h in Blockpuffer überführt werden. Nach der Inkubation mit OvalbuminAntikörper wurde das Substrat auf die Membran pipettiert und die Lichtreaktion mittels einer CCDKamera aufgenommen. Um die adjuvante Wirkung der Nanopartikel und der UV-inaktivierten Viren in Form einer Aktivierung von Antigen-präsentierenden Dendritischen Zellen zu überprüfen wurden je 5x105 unreife DZ mit 1 µg/ml LPS als Positivkontrolle, 10 ng löslichem Ova sowie den unterschiedlichen Partikelpräparationen inkubiert. Es wurden sowohl unbeladene Partikel verwendet, um eine mögliche adjuvante Wirkung der Partikel an sich zu belegen, als auch mit je 10 ng Ova beladene Partikel. Zudem kamen 109 virale Partikel des aktiven AdVpIX-OvapIX-Ova sowie des UV-inaktivierten AdVpIX-Ova zum Einsatz. Nach 16 h Inkubation wurden die Oberflächenmarker CD80 und CD86 – beides Aktivierungsmarker Dendritischer Zellen - eingesetzt und durchflusszytometrische Analysen durchgeführt. Die Basisexpression unreifer DZ war gering: es traten nur 66 bzw. 54 % für CD80 bzw. CD86 positive Zellen auf (Abb. 3.5.2). Im Vergleich dazu zeigte sich mit 85 bzw. 75 % bei der Positivkontrolle LPS eine signifikant höherere CD80 bzw. CD86 Expression als bei unaktivierten DZ (p<0,05, Dunn's-Post hoc-Methode). Auch bei mit Viren inkubierten Zellen fand sich eine Ergebnisse 67 Hochregulation der Expression auf 77-79 % (p<0,05, Dunn's post-hoc Methode), wobei der der prozentuale Anteil bei aktivem und inaktivem Virus statistisch nicht unterschiedlich war. Gegenüber der Kontrolle wiesen auch die mit 340POva inkubierten Zellen sowie im Falle von CD86 die 200POva eine statistisch signifikante Erhöhung der Expression auf. CD80+ % positive Zellen 100 90 CD86+ * * * ** ** ** 80 70 60 50 DZ LPS Ova a P Ov 24 4P 2 P Ov 60 0P 6 a a P Ov 93 3P 9 0P O 22 20P 2 va va va 0P O X-O IX-O p 34 40P pI a dV 3 v A -O IX p V Ad va Abb. 3.5.2: Durchflusszytometrische Analyse der Hochregulation der DC-Aktivierungsmarker CD80 und CD86 5x105 DZ wurden zusammen mit 10 ng löslichem Ova, 1 µg/ml LPS, unbeladenen Partikeln, mit 10 ng Ova-beladenen Partikeln, 109 VP AdVpIX-OvapIX-Ova sowie 109 AdVpIX-Ova für 16 h inkubiert. Die anschließende FACS-Analyse des prozentualen Anteils an CD80 und CD86, zwei Oberflächenmarker die bei Aktivierung der Zelle hochreguliert werden, zeigte bei der Positivkontrolle LPS sowie den beiden Viruspräparationen einen signifikant höheren Anteil an CD86 im Vergleich zu unbehandelten DZ mit *= p<0,05 zu unbehandelten DZ (Dunn’s post-hoc Methode). Weitergehend sollte untersucht werden, ob die Interferon-Produktion der Zellen angeregt wurde. Dafür wurden je 100 µl des jeweiligen Zellüberstandes in einem Interferon α (IFNα) bzw. β (IFNβ) spezifischen ELISA eingesetzt. Die Basisproduktion von Interferon α sowie β durch unreife Dendritischen Zellen lag unter 10 pg/ml (Abb. 3.5.3). In keinem Fall wurde bei den mit Partikeln inkubierten Zellen ein signifikanter Anstieg in der Zytokinproduktion nachgewiesen, wobei die Werte bei Proben mit unbeladenen Partikeln unterhalb der Basisproduktion lagen und aus diesem Grund nicht dargestellt sind. Bei Inkubation der Zellen mit Virus - unabhängig ob in aktiver oder inaktiver Form - produzierten die DZ mit Werten zwischen 196-208 pg/ml signi- Ergebnisse 68 fikant mehr Interferon α und β als unstimulierte Zellen (p<0,05, Student-Newman- IFN [pg/ml] Keuls-Methode). * * 250 200 150 30 * * IFN α IFN β 20 10 va A dV pI XO va pI XO IX -O A dV p sl lö va O 34 0P va O 22 0P va va O 93 P va 60 P O va O P 24 ic he s D O va C s >1 0 Abb. 3.5.3: Menge an Interferon α und β im Überstand von Dendritischen Zellen nach Inkubation mit löslichem Ova, Ova-beladenen Partikeln unterschiedlicher Größe, AdVpIX-OvapIX-Ova sowie AdVpIX-Ova 5x105 DZ wurden zusammen mit 10 ng löslichem Ova, unbeladenen Partikeln, 10 ng Ova beladenen Partikeln, 109 viralen Partikeln AdVpIX-OvapIX-Ova oder AdVpIX-Ova für 16 h inkubiert. Anschließend wurden die Zellen abzentrifugiert. Von den Zellüberständen wurden je 100 µl in Interferon α bzw. β-spezifischen ELISAs eingesetzt, um die enthaltene Menge an Interferon zu bestimmen. Die beiden Viruspräparationen induzierten die Produktion von beiden Interferonen, was sich in einer signifikant höheren Menge im Vergleich zu unbehandelten DZ zeigte. *= p<0,05 zu unbehandelten DZ (StudentNewman-Keuls-Test). N=3 3.6 Ergebnisse der in vitro-Antigenpräsentation an CD8+ Zellen durch Antigenbeladene Dendritische Zellen Um zu überprüfen, ob die Nanopartikel sowie die Viren in der Lage sind, eine Proliferation von Ova-spezifischen CD8+ T-Zellen in vitro zu induzieren, wurden Dendritische Zellen mit der jeweiligen Probe für 5 h inkubiert. Parallel wurden die Lymphozyten einer OT-I Maus gewonnen, eine transgene Züchtung mit C57BL/6-Hintergrund, die sich durch Ova-spezifische CD8+ T-Zellen auszeichnet. Aus der Lymphozytenpopulation wurden mittels Magnetseparation die CD8+ Zellen isoliert, mit CFSE markiert und in einem Verhältnis von 1:4 für 72 h mit den Antigen-beladenen DZ inkubiert. Da CFSE an die Tochtergeneration weitergegeben wird, belegt eine Abnahme der Fluoreszenzintensität eine Proliferation der Zellen. Anschließend erfolgte die FACS Analyse der CD8+ Zellen. Eine Verschiebung in Richtung verminderter Ergebnisse 69 Fluoreszenzintensität spiegelt dabei die Teilung von spezifischen CD8+ T-Zellen wider (Abb. 3.6.1). Nach Inkubation von naiven Dendritischen Zellen mit den CD8+ T Zellen befanden sich nur 3,5 % OT-I Zellen im Zyklus (Abb. 3.6.2). Wurden die Dendritischen Zellen jedoch mit Ovalbumin beladen, führte die Inkubation zusammen mit den T-Zellen zu einer Verschiebung der Histogrammkurve in Richtung schwächerer Fluoreszenzintensität und damit zu einem höheren Prozentsatz an OT-I T-Zellen im Zyklus; also zu einer Proliferation der T-Zellen. Der Anstieg auf 32,5 % war im Vergleich zur Kontrolle statistisch signifikant (p<0,05, Student-Newman-Keuls-Methode). Dies traf auch für die Proben mit Ova-beladenen Partikeln zu, wobei der prozentuale Anteil im Mittel bei 35 % OT-I Zellen im Zyklus lag. Nicht signifikant erhöht war der prozentuale Anteil bei Inkubation mit unbeladenen Partikeln. Auch die Viren – sowohl in aktiver als auch inaktivierter Form – riefen eine Proliferation der CD8+ T-Zellen hervor, wobei im Mittel 34 % T-Zellen sich geteilt hatten. Es konnte kein Unterschied in der Fähigkeit zur Induktion der Proliferation festgestellt werden, wenn das Virus einer UV-Inaktivierung unterzogen wurde. 45 Count 34 23 11 4 0 10 0 CD8 APC 10 CD8+ T-Zellen 3 10 1 10 2 10 CFSE 3 10 4 10 2 10 34 1 10 0 256 512 768 1024 FSC-H Count 26 0 10 17 9 0 0 10 1 10 2 10 CFSE 3 10 Abb. 3.6.1: Selektionsstrategie zur Messung der Zellproliferation Lymphozyten wurden nach Granularität und Dichte ausgewählt. Nur CD8 positive Zellen wurden bei der Messung berücksichtigt. Eine Verschiebung in Richtung verminderter Fluoreszenzintensität spiegelt dabei die Teilung von spezifischen CD8+ T-Zellen wieder (rechts unten). 4 10 % OT-I Zellen im Zyklus Ergebnisse 70 60 * * * * * * * 40 20 va pI XO va A dV p A dV pI XO O va IX -O va 34 0P 34 0P O va 22 0P 22 0P O va 93 P 93 P O va 60 P 60 P O va 24 P 24 P va O he s lic lö s K on tr o lle 0 Abb. 3.6.2: In vitro Proliferation von Ova-spezifischen CD8+ T Zellen nach Inkubation mit Antigen-beladenen Dendritischen Zellen Dendritische Zellen wurden mit Antigen beladen, für 72 h mit CFSE-markierten CD8+ T Zellen einer OT-I Maus inkubiert und anschließend einer FACS-Analyse unterzogen. Die Zellen wurden anhand ihrer Größe und Granularität ausgewählt, auf CD8+ selektiert und die Fluoreszenz bestimmt. Da CFSE an die Tochtergeneration weitergegeben wird, belegt eine Abnahme der Fluoreszenzintensität eine Proliferation der Zellen (A, rechts oben). Im Falle von löslichem Ova, mit Ova-beladenen Partikeln, AdVpIX-OvapIX-Ova sowie AdVpIX-Ova kam es zu einer signifikanten Steigerung der CD8+ T Zellzahl (p<0,05, Student-Newman-Keuls-Methode). Dies traf für unbeladene Partikel nicht zu . 3.7 Einfluss verschiedener Endozytose-Inhibitoren auf die zellulären Aufnahme von löslichem Protein, beladenen Nanopartikeln sowie Adenoviren Um Unterschiede in den Aufnahmewegen von Protein, Nanopartikel und viralen Partikeln und somit einen möglichen Rückschluss über Prozessierungsvorgänge machen zu können, wurden Dendritische Zellen generiert und mit Endozytose-inhibitoren inkubiert. Chloropromazin verhindert die Ver- und Entnetzung von Clathrin, einem Protein, das die Clathrin-vermittelte Endozytose bewirkt. Auch Cytochalasin D wirkt hemmend, indem es die F-Aktin-Elongation blockiert und somit das Aktin-Zytoskelett destabilisiert. Genestein wirkt spezifisch gegen Tyrosin-Proteinkinasen und verhindert so die Caveolae-vermittelte Endozytose. Für jede einzelne Probe wurde eine Referenzmessung durchgeführt, bei der unbehandelte Zellen verwendet wurden. Hiernach wurde die Anzahl an Zellen, die Protein, Partikel bzw. Viren aufgenommen haben ermittelt 100 % gesetzt. Ergebnisse 71 Bei löslichem Protein ließ sich keine reduzierte Aufnahme feststellen (Abb. 3.7.1). Bei mit 24POva inkubierten Zellen hingegen kam es sowohl bei Chloropomazin als auch Cytochalasin D zu einer Reduktion der Aufnahme von fast 50 %. Bei 60POva und 93POva hemmten beide die Endozytose, wobei Chloropromazin auch bei 220POva und 340POva die höchste Hemmung hervorrief und somit die Aufnahme über Chlathrin-Vesikel verhinderte. Beide beeinflussten die Aufnahme von AdVpIX-OvapIXOva nicht, AdVpIX-Ova wurde jedoch nur halb soviel aufgenommen wie ohne Inhibitoren. Genestein als Blocker Caveolae-vermittelter Aufnahme beeinflusste die Endozytose nicht. Chloropomazin Cytochalasin D Genestein % zelluläre Aufnahme 400 300 200 150 100 50 0 lösliches Ova 24POva 60POva 93POva 220POva 340POva AdVpIX-Ova AdVpIX-OvapIX-Ova Abb. 3.7.1: Analyse der Endozytose-Inhibition durch Chloropromazin, Cytochalasin D und Genestein 106 unreife Dendritische Zellen wurden mit Chloropromazin (7,5 µg/ml), Methyl-β-Cyclodextrin (20 mM), Cytochalasin D (2 µg/ml) bzw. Genestein (200 mM) für 1 h vorinkubiert. Als Positivkontrolle wurden unbehandelte DZ ausplattiert. Anschließend erfolgte die Inkubation der Zellen mit 100 ng löslichem Ova, je 2 µl der Ova-beladenenen Partikel bzw. 2x1010 VP AdVpIX-OvapIX-Ova und AdVpIX-Ova. Die Analyse erfolgte mittels Durchflusszytometrie, wobei die Werte der Positivkontrolle (Zellen, die mit Probe jedoch ohne Inhibitoren inkubiert wurden) auf 100 % gesetzt und der prozentuale Anteil der Aufnahme durch inhibitorisch beeinflusste Zellen bestimmt wurde. N=3. 3.8 Einfluss der Proteinmenge auf die Immunantwort gegen lösliches Ova und Ova-beladene 93 nm Partikel Um den unterschiedlichen Effekt von löslichem Protein und dem an Nanopartikel gebundenen Protein auf die Antikörperantwort näher zu untersuchen, sollten verschiedene Proteinmengen miteinander verglichen werden. Die Bestimmung der humoralen Immunantwort 2 Wochen nach intramuskulärer Applikation ergab für den IgG1-Gehalt den höchsten Wert bei 93POva, die mit 5000 ng beladen waren (Abb. 3.8.1 A). Bei IgG2a lag kein signifikanter Unterschied der Proben zum Serum naiver Kontrolltiere vor (Abb. 3.8.1 B). Der IgG1-Wert von Tieren, die mit 500 ng 93POva Ergebnisse 72 immunisert worden waren, lag bei 7x105 RLU/s, bei Immuniserung mit der 10fachen Menge an löslichem Protein jedoch nur bei 9x104. Dies lässt darauf schließen, dass Protein an Nanopartikel gekoppelt weitaus effektiver bei Immunisierungen ist als in löslicher Form. # A * * 1.0×10 6 1.0×10 7 * RLU/s [log10] 1.0×10 5 1.0×10 4 1.0×10 3 1.0×10 6 1.0×10 5 1.0×10 4 ng ng 0 50 00 50 O va O va va 50 ng ng 00 O 50 ng O 93 P va 50 0 O va 50 ng ai v N va 93 P O va 93 P O ng 50 00 ng O va 50 O ng va 50 0 O ng va 50 00 ng 0 ng 50 va O 93 P 93 P O va 50 N ai v 1.0×10 3 93 P RLU/s [log10] 1.0×10 7 B Abb. 3.8.1: Humorale Immunantwort der Antikörper Subklassen IgG1 und IgG2a 14 Tage nach Immunisierung wurde retrobulbär Blut entnommen, das Serum gewonnen und Ovaspezifische Antikörper der Subklassen IgG1 (A) und IgG2a (B) mittels eines Antikörper-ELISAs bestimmt (1:100 Verdünnung). Statistisch signifikante Unterschiede wurden mit *= p<0,05 gegen das Serum naiver Tiere bzw. untereinander mit # gekennzeichnet (Student-Newman-Keuls-Methode). N=4 3.9 Ermittlung der geeigneten Applikationsroute für Antigen-beladene Nanopartikel Um die Nanopartikel gut mit adenoviralen Partikeln zu vergleichen, musste zunächst die optimale Applikationsroute für Erstgenannte evaluiert werden, indem sowohl die Antikörperlevel als auch die zelluläre Immunantwort untersucht wurden. Die Injektion von 5 µg löslichem Ova bzw Ova-beladenen Partikeln induzierte 14 Tage nach Immunisierung unabhängig von der gewählten Applikationsweise Ova-spezifische Antikörper, wobei zunächst der Gesamt-Ig Gehalt der Immunseren mittels ELISA ermittelt wurde (Abb. 3.9.1). Für die kleineren Partikel bis 60 nm schien sich in Bezug auf die Produktion von IgG Antkörpern insbesondere die intramuskuläre und intraperitoneale Injektion zu eignen, bei mit 93POva immunsierten Tieren wurde die höchste Antikörperantwort bei intramuskulärer und plantarer Applikation verzeichnet. Während bei der Gruppe, die 220POva erhielt, keine Tendenz für die beste Route festgestellt werden konnte, war die Antikörperantwort auch bei 340 nm Partikel intra- Ergebnisse 73 muskulärer sowie plantarer Applikationsroute am höchsten. Die subkutane Applikation erbrachte insgesamt die geringste Antikörpermenge. Naiv 2.0×10 6 24POva 60POva 93POva 220POva # * * in tr am us ku lä r 0 * # *# * * # # # *# * *# * * # * * * 340POva lösliches Ova on ea l 5.0×10 5 # ra pe rit * * in t # # # # 6 r 1.0×10 * * pl an ta RLU/s * # # # su bk ut an * 1.5×10 6 Abb. 3.9.1: Humorale Immunantwort 14 Tage nach Immunisierung mit Ova-beladenen Nanopartikeln bzw. löslichem Ova 14 Tage nach Immunisierung wurde retroorbital Blut entnommen, das Serum gewonnen und die Konzentration Ova-spezifischer IgG Antikörper mittels eines Antikörper-ELISAs bestimmt (1:10000 Verdünnung des Serums). Statistisch signifikante Unterschiede wurden mit *= p<0,05 gegen das Serum naiver Tiere und #= p<0,05 gegen lösliches Ova (Student-Newman-Keuls-Methode) gekennzeichnet. N=6 Die Evaluation der zellulären Immunantwort erfolgte 14 Tage nach der Immunisierung. Den Tieren wurde die Milz entnommen, und die Lymphozyten ex vivo mit Ova-spezifischen Peptiden für 6 h stimuliert. Anschließend wurde die Produktion von Zytokinen durch CD8+ und CD4+ T-Zellen per FACS-Analyse untersucht. Die 93POva sowie die größeren Partikel induzierten keine zelluläre Immunantwort, der prozentuale Anteil CD8+IFNγ+CD107+ Zellen unterschied sich nicht signifikant von dem naiver Tiere (Abb 3.9.2 B). Die 24POva bzw. 60POva hingegen regten zumindest die Zytokinproduktion an, wobei es nur zu einem signifikanten Unterschied bei plantarer (p<0,05, Student-Newman-Keuls-Methode), bzw bei 24POva auch bei intramuskulärer Applikation kam (p<0,05, Student-Newman-Keuls-Methode). Es konnten auch polyfunktionale Zellen detektiert werden (Abb. 3.9.2 C). Ergebnisse 74 A 1024 4 10 10 4 0,24% 0,10% CD8+ Lymphozyten 3 Lymphozyten 256 10 10 CD107 FITC 512 CD8 PerCP SSC-Height 768 CD107+/IFNy+ 2 10 10 3 2 1 10 0 10 0 10 10 1 0,06% 0 0 B 256 512 FSC-Height % IFNγ + /CD8+ 10 1024 intramuskulär 0.8 0.6 768 0 0 256 512 768 FSC-Height 1024 * 10 2 IFNg PE 10 3 10 4 intraperitoneal subkutan plantar * 10 1 * 0.4 0.2 va 22 0P O va lö 34 sl 0 P O ic va he s O va va O P 93 va O O P P 60 24 va va O PO va va 22 0 lö 34 sl 0 ic he s PO va O P 93 va O O P P 60 24 va 22 0P O va lö 3 4 sl 0 P O ic va he s O va va O P 93 va O O P P 60 24 N a 24 i v PO va 60 PO va 93 PO va 22 0P O va lö 3 4 sl 0 P O ic va he s O va 0.0 * 0.20 0.15 0.10 * * 0.05 24 PO va 60 PO va 93 PO va 22 0P O va lö 34 sl 0P O ic va he s O va 24 PO va 60 PO va 93 PO va 22 0P O va lö 34 sl 0P O ic va he s O va 24 PO va 60 PO va 93 PO v a 22 0P O v a lö 34 sl 0P O ic va he s O va 0.00 N a 24 iv PO va 60 PO va 93 PO va 22 0P O va lö 34 sl 0P O ic va he s O va % (IFNγ + IL-2+ CD107a+ )/ CD8+ Zellen C Abb. 3.9.2: CD8+ T-Zell vermittelte Immunität in Abhängigkeit von der Partikelgröße und Applikationsroute Milzzellen immunisierter Tiere wurden 14 Tage nach Immunsierung ex vivo mit dem Peptid SIINFEKL für 6 h stimuliert und anschließend gegen CD8, die Zytokine IFNγ, IL-2 bzw. den Degranulationsmarker CD107a gefärbt. Es wurden nur Zellen in die Messung einbezogen, die einer bestimmten Größe und Granularität entsprachen und die CD8+ waren. Durch die 3fach Färbung konnten 1fach, 2fach und 3fach positive Zellen separat voneinander analysiert werden (A). Nur die 24POva und 60POva induzierten IFNγ produzierende Zellen (B), und nur die 24POva konnten mehrfach polyfunktionale CD8+ T-Zellen induzieren (C). Die Werte entsprechen der Differenz aus den Werten stimulierter und unstimulierter Zellen. Statistische Signifikanz mit *=p<0,05 gegen Naiv (Student-Newman-Keuls-Methode). N=-3-4 Ergebnisse 75 Sowohl bei den Tieren, die mit 24POva als auch 60POva immunisiert wurden, wurde ein signifikanter Anstieg der IFNγ produzierenden CD4+ T-Zellen verzeichnet (Abb. 3.9.3). Während der Wert naiver Tiere bei 0,01 % lag, produzierten im Falle der intramuskulären Applikation 0,1 % bei 24POva bzw. 0,15 % bei 60POva der CD4+ Zellen IFNγ (p<0,05, Student-Newman-Keuls-Methode). Bei plantarer, subkutaner sowie intraperitonealer Applikation waren die Werte der beiden Gruppen zudem im Vergleich zu naiven Tieren signifikant höher (p<0,05, Student-Newman-Keuls-Methode). Der höchste Wert wurde bei Tieren der 24POva Gruppe bei plantarer Applikation der Partikel mit einem Prozentsatz von 0,21 % IFNγ produzierenden Zellen gemessen. Aufgrund dieser Ergebnisse wurde die plantare Applikation für alle weiteren Versuche gewählt. intramuskulär %IFNγ + /CD4+ Zellen 0.3 * * * plantar * intraperitoneal subkutan * * * * 0.2 0.1 24 PO va 60 PO va 93 PO va 22 0P O v a lö 34 sl 0P O ic va he s O va 24 PO va 60 PO va 93 PO va 22 0P O va lö 34 sl 0P O ic va he s O va 24 PO va 60 PO va 93 PO va 22 0P O va lö 34 sl 0P O ic va he s O va N a 24 iv PO va 60 PO va 93 PO va 22 0P O va lö 34 sl 0P O ic va he s O va 0.0 Abb. 3.9.3: CD4+ T-Zell vermittelte Immunität in Abhängigkeit von der Partikelgröße und Applikationsroute Milzzellen immunisierter Tiere wurden 14 Tage nach Immunsierung ex vivo mit drei Ova-spezifischen Peptiden für 6 h stimuliert und anschließend gegen CD4 und IFNγ gefärbt. Die Selektionsstrategie beinhaltete Zellen bestimmter Größe und Granularität, die CD4+ waren. Nur die 24POva und 60POva induzierten IFNγ produzierende CD4+ Zellen. Die Werte entsprechen der Differenz aus den Werten stimulierter und unstimulierter Zellen. Statistisch signifikante Unterschiede mit *=p<0,05 (StudentNewman-Keuls-Methode). N=4 3.10 Vergleichende Analyse der Immunantwort nach Immunisierung mit löslichem Ovalbumin, Ovalbumin-beladenen Partikeln, AdVpIX-Ova und AdVpIXOvapIX-Ova Um einen direkten Vergleich zwischen den immunstimulatorischen Fähigkeiten der verschiedenen Proteinvakzine zu erhalten, wurden C57BL/6 Mäuse mit löslichem Protein, Antigen-beladenen Partikeln, UV-inaktiviertem Virus sowie als Positiv- Ergebnisse 76 kontrolle mit aktivem Adenovirus immunisiert. In vorhergehenden Experimenten wurde festgestellt, dass 1010 virale Partikel des Virus AdVpIX-OvapIX-Ova ungefähr 50 ng Ovalbumin in Form des pIX-Ova Fusionsproteins auf ihrer Oberfläche präsentieren. Dementsprechend wurden die Präparationen so eingestellt, dass jedes Tier insgesamt 50 ng Ovalbumin plantar in die Fußsohle erhielt. Um den Einfluss der Nanopartikel- bzw. Virusgröße mit einzubeziehen, wurden die folgenden Gruppen gewählt: 24POva, 93POva, 340POva, AdVpIX-OvapIX-Ova, AdVpIX-Ova, lösliches Ova. Es wurde zweimal im Abstand von drei Wochen immunisiert. Anschließend wurden wie zuvor beschrieben Antikörper und T-Zellantwort bestimmt (Abb. 3.10.1). 24POva 93POva 340POva AdVpIX‐OvapIX‐Ova AdVpIX‐Ova Woche 0 1 24Ova 93POva 340POva AdVpIX‐OvapIX‐Ova AdVpIX‐Ova 2 3 Antikörper 4 5 6 Antikörper +Zytokinfärbung Abb. 3.10.1 Immunisierungsschema Die Tiere wurden im Abstand von drei Wochen zweimal mit Ova-beladenen Partikeln, aktiven und inaktivierten Viren immunisiert, wobei jeweils eine Gesamt-Menge von 50 ng Ovalbumin eingesetzt wurde. Zu zwei Zeitpunkten wurden Antigen-spezifische Antikörper im Serum der Tiere bestimmt, am Ende des Versuchs erfolgte die Milzentnahme und die Bestimmung Zytokin-produzierender CD8+ TZellen nach spezifischer Stimulation. Schon drei Wochen nach der ersten Immunsierung ließ sich nach Applikation von 1010 viralen Partikeln des aktiven sowie inaktivierten Virus ein Anstieg der AntikörperKonzentration verzeichnen, wobei sowohl Antikörper der Subklasse IgG1 als auch IgG2a induziert wurden (Abb. 3.10.2 A, B, C). Diese Antikörperspiegel waren signifikant erhöht im Vergleich zum Serum naiver Tiere und dem Serum der anderen Gruppen (p<0,05, Student-Newman-Keuls-Methode). Die Seren der mit Partikeln immunisierten Tieren wiesen keine signifikante Steigerung zu denen naiver Tiere auf. Nach einer Auffrischungs-Immunisierung wurden -- mit Ausnahme von Seren der mit löslichem Ovalbumin immunisierten Tiere -- signifikant höhere Antikörperantworten Ergebnisse 77 ermittelt (Abb. 3.10.2 E) Mit Ausnahme der Seren der mit 93POva immunsierten Tiere ergab sich für die AdVpIX-Ova Gruppe ein signifikanter Unterschied zu allen anderen (p<0,05, Student-Newman-Keuls-Methode). 3 Wochen nach der 1. Immunisierung A * 1.0×10 08 * 1.0×10 7 1.0×10 1.0×10 1.0×10 06 1.0×10 5 1.0×10 05 1.0×10 4 1.0×10 04 E * 1.0×10 07 * 1.0×10 06 1.0×10 05 1.0×10 05 1.0×10 04 1.0×10 04 1.0×10 03 1.0×10 03 F * 1.0×10 07 * * 1.0×10 07 1.0×10 06 1.0×10 08 * * * * 1.0×10 08 * * * 1.0×10 07 1.0×10 06 va pI XO va A dV XO va 0P IX -O va p I O va va O 34 dV p A es N va A dV pI X -O va pI XO O A dV p IX -O va O 34 0P 93 P O lö N sl ai ic v he s O va 24 P 93 P 1.0×10 03 O 1.0×10 03 24 P 1.0×10 04 ai v 1.0×10 04 va 1.0×10 05 va 1.0×10 05 O va 1.0×10 06 va RLU/s [log 10] 1.0×10 08 lic h RLU/s [log 10] 1.0×10 08 C * 6 1.0×10 3 B * 07 lö s RLU/s [log 10] 1.0×10 8 3 Wochen nach der 2. Immunisierung D Abb. 3.10.2: Humorale Immunantwort nach Immunisierung mit löslichem Ova, Ova-beladenen Partikeln, aktivem und inaktivertem Adenovirus 3 Wochen nach der ersten (A-C) sowie zweiten (D-F) Immunisierung wurde den C57BL/6 Mäusen retrobulbär Blut entnommen, das Serum gewonnen und Ova-spezifische Antikörper bestimmt. Sowohl der totale Anteil an Immunoglobulinen (A,D) sowie Immunoglobulinen der Subklassen IgG1 (B, E) und IgG2a (C, F) wurde mittels eines Antikörper-ELISAs bestimmt (1:100 Verdünnung). Statistisch signifikante Unterschiede wurden mit *= p<0,05 gegen das Serum naiver Tiere gekennzeichnet (StudentNewman-Keuls-Methode). N=8 Ergebnisse 78 Die Milzentnahme und Untersuchung der T-Zell-Antwort erfolgte 3 Wochen nach der zweiten Immunisierung. Durch die Immunisierung mit aktiven AdVpIX-OvapIX-Ova wurden polyfunktionale Zytokin-produzierende CD8+ sowie CD4+ T-Zellen induziert. Während bei naiven Tieren im Mittel nur 72 CD8+ IFNγ+ CD107a+ Zellen auftraten, lag der Wert bei aktivem Virus bei 12310 Zellen (Abb. 3.10.3 A). Mit Ausnahme von den mit 340POva immunisierten Tieren konnte in allen andern Gruppen zumindest in einigen Tieren ein Anstieg in der Zellpopulation verzeichnet werden, dieser war aber aufgrund der Gruppenvarianz nicht signifikant. Der Wert der mit aktivem Virus immunsierten Tieren war zusätzlich signifikant höher als der der mit löslichem Ova, 93POva sowie 340POva immunisierten Tiere. Auch im Falle von doppelt positiven CD4+ IFNγ+ TNFα+ T-Zellen fand sich ein signifikant höherer Anteil bei Virus-immunisierten Tieren im Vergleich zu naiven Tieren (Abb. 3.10.3 B). Zudem lag der Wert von 638 Zellen signifikant höher als der aller anderen Gruppen. Um eine mögliche Tendenz in Richtung einer TH2-Immunantwort näher zu untersuchen, wurden Zellen mit Ovaspezifischen Peptiden über Nacht inkubiert und anschließend die IL4 Konzentration in einem ELISA bestimmt. Hierbei produzierten nur die Zellen der Virusimmunisierten Tiere IL-4, zumindest in ausreichender Menge um mit dem ELISA quantifiziert zu werden (Abb.3.10.3 C). Dieser Unterschied war nicht nur gegen den Überstand der naiven Gruppe signifikant, sondern auch zu dem aller anderen Gruppen. Die mittlere Konzentration lag bei AdpIX-Ova bei 2,0 pg/ml, bei dem exprimierenden Virus AdVpIX-OvapIX-Ova bei 5,7 pg/ml.. Ergebnisse 79 B dV pI XO va va va A A A O lö sl A dV dV p IX -O va N ai ic v he s O va 24 P va va 0 pI XO va IX -O O va O O lö sl 34 0P IX -O va p 93 P va 0 200 O 200 400 va 400 600 O 600 800 dV 34 0P pI XO va p 800 * 1000 93 P Anzahl (IFNγ + TNFα +) Zellen/ 106 CD4+ Zellen * 30000 20000 10000 N ai ic v he s O va 24 P Anzahl (IFNγ + CD107a+ ) Zellen/ 106 CD8+ Zellen A C * IL-4 [pg/ml] 25 15 10 * 8 6 4 2 va A dV IX -O pI XO va va O va O 34 0P IX -O va p dV p 93 P A lö s O N ai lic v he s O va 24 P va 0 Abb.3.10.3: Intensität der zellulär vermittelten Immunität bei löslichem Ova, Ova-beladenen Partikeln unterschiedlicher Größe, aktivem AdVpIX-OvapIX-Ova und UV-inaktiviertem AdVpIX-Ova Milzzellen immunisierter Tiere wurden 3 Wochen nach der zweiten Immunsierung ex vivo mit Ovaspezifischen Peptiden für 6 h (A,B) bzw. über Nacht (C) stimuliert. Anschließend erfolgte eine Färbung gegen CD8, IFNγ und CD107a (A) bzw. CD4, IFNγ undTNFα (B), oder der Überstand der Zellen wurde abgenommen und ein quantitativer IL-4 ELISA durchgeführt (C). Bei Tieren, die mit 1010 viralen Partikeln von AdVpIX-OvapIX-Ova immunisiert wurden konnte ein signifikanter Anstieg in zweifach Zytokin-produzierenden CD8+ und CD4+ T-Zellen sowie der produzierten IL4-Menge im Vergleich zu naiven Tieren nachgewiesen werden. Auch bei der AdpIX-Ova Gruppe war die Menge an IL-4 signifikant höher (*= p<0,05; Dunn’s Post-hoc-Methode). Statistisch signifikante Unterschiede gegen Zellen nichtimmunisierter Tiere wurden mit einem Sternchen (*) gekennzeichnet (p<0,05; Dunn’s Post-hocMethode). N=8. Ergebnisse 80 3.11 Abhängigkeit der Antikörperproduktion und der Induktion zytotoxischer CD8 T-Zellen von der CD4+ T-Zellpopulation Um eine mögliche T-Zell unabhängige Aktivierung von B-Zellen sowie den Einfluss der CD4+ T-Zellpopulation auf die CD8+ T-Zellantwort zu untersuchen, wurden die Tiere zum Zeitpunkt beider Immunisierungen nach dem in Abb. 3.11.1 aufgeführten Schema mit Anti-CD4-Antikörpern behandelt, wodurch die CD4+ T-ZellPopulation depletiert wurde. 24POva 93POva 340POva AdVpIX-Ova AdVpIX-OvapIX-Ova 24POva 93POva 340POva AdVpIX-Ova AdVpIX-OvapIX-Ova CD4-Depletion Tag -3 -1 0 1 3 5 18 20 21 Antikörper 22 24 26 42 Antikörper +Zytokinfärbung Abb. 3.11.1: Immunisierungs- und Depletionsschema Den Tieren wurden zu bestimmten Zeitpunkten vor und nach den Immunisierungen mit Partikeln und Adenoviren intraperitoneal Anti-CD4-Antikörper appliziert, wodurch die CD4 T-Zell-Population depletiert wurde. Die Depletionseffizienz wurde mittels FACS-Analyse überprüft. Während es sich bei 14,25 % bzw.35,92 % der Lymphozyten in der Milz bzw. Lymphknoten einer naiven Maus um CD4+-Zellen handelte, fand sich schon nach dreimaliger Applikation von 125 µl Hybridoma-Überstand nur noch ein Prozentsatz von 0,02 % CD4+ TZellen (Abb.3.11.2 A). Die Antikörperbestimmung brachte nach der ersten Immunisierung keine signifikante Erhöhung im Vergleich zum Serum naiver Tiere (Daten nicht gezeigt). Auch nach der zweiten Immunsierung wurde keine signifikante Steigerung der Subtypen IgG1 und IgG2a verzeichnet (Abb. 3.12.2 B, C). Ergebnisse 81 unbehandelt SSC-H A 1024 1024 1024 768 768 512 512 256 SSC-H 768 0 10 512 mit Anti-CD4Antikörper behandelt 256 85,75% 0 10 14,25% 1 10 2 10 3 4 10 0,02% 99,98% 0 10 0 10 1 10 2 10 3 1 10 2 10 3 10 4 10 4 αCD4 256 Lymphozyten 1024 1024 768 768 512 512 0 256 512 FSC-H 768 1024 SSC-H 0 256 256 64,08% 0 10 0 10 35,92% 1 10 2 10 3 10 99,98% 0 4 10 0 0,02% 10 αCD4 B C 1.0×10 6 RLU/s [log 10] 1.0×10 5 1.0×10 4 1.0×10 3 1.0×10 5 1.0×10 4 va pI XO va dV p IX -O va pI XO dV O va A O va A 34 0P 93 P O va 24 P va va pI XO pI XO O A dV A dV pI XO va 34 0P va va O 93 P va O 24 P N ai v 1.0×10 3 N ai v RLU/s [log 10] 1.0×10 6 Abb. 3.11.2: Humorale Antwort gegen Ovalbumin nach Depletion der CD4+ T-Zell-Population Die Analyse der Milz- sowie Lymphknotenzellen zeigte eine Reduktion der CD4+ T-Zell-Population um 99,98% (A). 3 Wochen nach der zweiten Immunisierung mit Ovalbumin-beladenen Partikeln und Adenoviren wurde den Tieren retrobulbär Blut entnommen und das Serum (1:100 Verdünnung) auf Ovalbumin-spezifische Antikörper der Subtypen IgG1 (B) und IgG2a (C) analysiert. N=6 bzw. N=3 bei der AdVpIX-OvapIX-Ova-Gruppe. Die Untersuchung der zellulären Immunantwort in Form von Ova-spezifischen CD8 T-Zellen ergab einen signifikant höheren Anteil polyfunktionaler Zellen, die sowohl IFNγ als auch den Degranulationsmarker CD107a produzierten (Abb. 3.11.3). Dabei war eine gemittelte Zellzahl von 3423 CD8+IFNγ+CD107a+ bei AdVpIX-Ova sowie 27553 bei AdVpIX-OvapIX-Ova singifikant höher im Vergleich zu der Zellzahl naiver Tiere die im Mittel bei 64 CD8+IFNγ+CD107a+ lag. 82 * 50000 * 30000 10000 1500 1000 500 va A dV pI XO va XO 34 dp 0 PO va IX -O va p I O 93 P A O 24 P N va va 0 ai v Anzahl (IFNγ + CD107a+ ) Zellen /106 CD8+ Zellen Ergebnisse Abb. 3.11.3 Intensität der CD4-unabhängigen CD8+ T-Zellantwort nach CD4-Depletion zum Zeitpunkt der Immunisierungen Milzzellen immunisierter Tiere wurden 21 Tage nach Immunsierung ex vivo mit 3 Ova-spezifischen Peptiden für 6 h stimuliert und anschließend durchflusszytometrisch analysiert. Die Selektionsstrategie beinhaltete Zellen bestimmter Größe und Granularität, die CD8+ waren. Nur die Immunisierung mit AdpIX-OvapIX-Ova bzw. AdVpIX-Ova induzierte IFNγ und CD107a produzierende CD8+ Zellen. Statistisch signifikante Unterschiede mit *=p<0,05 gegenüber Naiv (Dunn’s post-hoc Methode). N=6 bzw. N=3 im Falle der AdVpIX-OvapIX-Ova immunisierten Mäusen. Diskussion 4 83 Diskussion Immunisierungen mit löslichem, rekombinantem Protein induzieren in den meisten Fällen nur schwache Immunantworten, so dass bei bereits angewendeten Vakzinen, z. B. gegen HBV, HPV und Influenza, auf die zusätzliche Gabe von Adjuvatien zurückgegriffen werden muss. Aus diesem Grund wurde versucht, Proteine zu immobilisieren, um eine bessere und längere Präsentation an Immunzellen zu erreichen. Beispielsweise wurden in ersten Versuchen Proteine auf eine Nitrozellulosemembran gegeben und Stücke davon in die Milz von Mäusen transplantiert, um so Antikörperreaktionen gegen das immobilisierte Protein hervorzurufen [173, 174]. Diese Methode war jedoch recht umständlich und wurde im Laufe der Jahre durch wirksamere Strategien ersetzt. In den letzten Jahren sind Partikel im Nanometerbereich immer mehr in den Fokus der Forschung geraten, da sie gute Immunantworten induzieren. Im Rahmen der vorliegenden Arbeit sollte daher untersucht werden, inwieweit die Immunantwort gegen das Modellantigen Ovalbumin differiert, wenn es als lösliches Protein, auf carboxylierte Polystyren-Nanopartikel gebunden oder auf der Oberfläche nicht mehr genexprimierender Adenoviren präsentiert wird. Die Beladung der Polystyren-Nanopartikel, deren Größe zwischen 24 nm und 340 nm lag, erfolgte zunächst mit aufgereinigten Proteinen [175]. Dabei war es wichtig, die Proteine im Überschuss anzubieten, um eine möglichst gleichmäßige und vollständige Bindung zu garantieren [175]. Außerdem mussten die Partikelmengen so gewählt werden, dass möglichst viel Protein auf möglichst wenigen Partikeln gebunden wurde, um anschließend keine Zytotoxizität zu beobachten. Bei detailierteren Studien anderer Arbeitsgruppen dazu wurde eine Größen- sowie Mengenabhängigkeit festgestellt, wobei insbesondere größere Mengen von Partikeln kleiner als 20 nm Zellschädigungen durch Apoptose und Nekrose induzierten. Je größer die Partikel waren, desto geringer war ihr zytotoxisches Potential, welches durch Beladung mit Protein zusätzlich noch verringert wurde [176]. Bei der Beladung zeigte sich weitergehend, dass sich die einzelnen Nanopartikelpräparationen unterschiedlich gut beladen ließen und auch die Beladungseffizienz unabhängiger Ansätze großen Schwankungen unterlag. Eine mögliche Ursache dafür kann die unterschiedliche Handhabung der verschiedenen Partikelgrößen gewesen sein. Während 93 nm Partikel sich nur schwer pelletieren ließen und der Verlust an Partikeln im Laufe des mehrmaligen Zentrifugierens nicht genau quantifiziert wurde, traten bei 60 Diskussion 84 nm Partikeln, die nicht durch Zentrifugation pelletiert, sondern über Aufreinigungssäulen gewaschen werden mussten, zum Teil Verklumpungen auf, die nur durch längere Ultraschallbehandlung behoben werden konnten. Um eine gute Immunantwort zu induzieren, ist eine Aufnahme durch Antigen-präsentierende Zellen und der Transport zu den nächstgelegenen Lymphknoten notwendig. Darum wurden im Rahmen der vorliegenden Arbeit zunächst in vitro Dendritische Zellen generiert und mit löslichen Ovalbumin sowie Ova-beladenen Partikeln inkubiert. Während bei 4°C kaum eine Aufnahme erfolgte, wurden bei 37°C signifikanten Mengen an Protein bzw. Partikeln von den Zellen internalisiert. Dass es sich dabei nicht um unspezifische Adsorption von außen an die Zelle handelte belegten konfokalmikroskopische Aufnahmen. Es war ersichtlich, dass es sich um eine spezifische Aufnahme der 93 nm, 190 nm sowie 390 nm Partikel handelte. Leider wurde bei 93 nm die Auflösungsgrenze des Kofokalmikroskops erreicht und 60 nm Partikel konnten nicht mehr von der Hintergrundfärbung unterschieden werden. Andere Studien mit anderen Nachweismethoden belegten jedoch auch die Aufnahme von Partikeln mit einer geringeren Größe als 60 nm [177]. Diese Ergebnisse stimmen mit älteren Untersuchungen überein, bei der die Aufnahme von Partikeln mit einem Durchmesser von 150-700 nm näher untersucht wurde und eine endozytotische Aufnahme sowohl über FACS-Analyse als auch Konfokalmikroskopie nachgewiesen wurde [178]. Im nächsten Schritt wurde der zelluläre Transport der Partikel zum nächstgelegenen lymphatischen Gewebe untersucht, da dieser gewährleistet sein muss, um eine Präsentation an T- und B-Zellen zu ermöglichen. Hierzu wurden fluoreszierende Partikel plantar in die Hinterpfoten von C57BL/6 Mäusen injiziert und 24 h später die poplietalen Lymphknoten als nächstgelegenes lymphatisches Gewebe herauspräpariert. Die Partikel wurden sowohl durch DZ, Makrophagen, B-Zellen und zu einem geringen Prozentsatz auch durch T-Zellen aufgenommen, wobei erstaunlicherweise DZ bei allen Partikelgrößen nur eine untergeordnete Rolle zu spielen schienen. Vielmehr waren es B-Zellen und Makrophagen, die Partikel internalisiert hatten. Dies ist in Einklang mit einer Studie zum Transport von 20nm großen Partikeln und VLPs (virus-like-particles), die beide eher mit B-Zellen assoziiert waren, da sie tiefer in den subkapsulären Bereich penetrierten und so in die Nähe der BZell-Follikel gelangten [177]. Partikel unter 100 nm sind klein genug, um durch die endothelialen Knotenpunkte in den interstitiellen Zwischenräumen in die lympha- Diskussion 85 tischen Gefäße vordringen und so innerhalb einiger Stunden in die Lymphknoten zu gelangen [177]. Falls es somit zu einem zellunabhängigen Transport der kleineren Partikel zu den Lymphknoten ohne Aufnahme durch einwandernde Zellen kommt, ist eine direkte Internalisierung durch Lymphknoten-residierende B-Zellen möglich. Größere Partikel verbleiben zum Teil an der Injektionsstelle, werden dort von einwandernden Zellen aufgenommen und zu den nächstgelegenen Lymphknoten transportiert. Auch diese größeren Partikel wurden größtenteils von B-Zellen und Makrophagen aufgenommen. Im Gegensatz dazu belegen andere Studien eine positive Korrelation der Größe der Partikel und der Aufnahme durch DZ bzw. eine negative Korrelation mit der Phagozytose durch Makrophagen [178]. Ein Problem bei diesem Test ist die Messbarkeitsgrenze mittels Durchflusszytometrie, da eine einzelne Zelle mehrere Partikel aufgenommen haben muss, um als positiv erkannt zu werden. Somit kann es sein, dass möglichweise Zellen, die vereinzelt Partikel aufgenommen hatten, nicht mit eingerechnet wurden. Dennoch wurde im Rahmen der vorliegenden Arbeit erfolgreich ein Vorhandensein von Partikeln aller Größen in den nächstgelegenen Lymphknoten nachgewiesen. In einem anderen Ansatz sollte die Immunogenität viraler Partikel in Form einer Proteinvakzine als weitere partikuläre Struktur untersucht werden. Um anschließend einen Vergleich zu den Nanopartikeln zu ermöglichen, mussten die viralen Vektoren zunächst modifiziert werden, indem durch UV-Inaktivierung die Genexpression beseitigt wurde. Der dafür verwendete Vektor AdVpIX-OvapIX-Ova [72] kodiert für ein Fusionskonstrukt aus dem adenoviralen Kapsidprotein pIX und Ovalbumin, welches C-terminal angehängt wurde. Durch die Fusion wird das Protein auf dem Viruskapsid präsentiert und sollte insgesamt laut Berechnungen 240fach je Virion vorhanden sein. Die 90minütige UV-Inaktivierung resultierte in einer Reduktion der Infektiösität um 5 Logstufen, was in Übereinstimmung zu den in der Originalpublikation der Methode beschriebenen Daten steht [167, 168]. Die noch verbleibende Genexpression nimmt jedoch keinen großen Einfluss auf die Immunantwort, wie eine Studie zur Dosisabhängigkeit zeigen konnte. Es wurde keine zelluläre und humorale Antwort nach Applikation von 107 und weniger infektiösen Adenoviren detektiert [179]. Weitergehend konnte im Rahmen der vorliegenden Arbeit keine Schädigung der Kapsid-Proteine nachgewiesen werden, da zum einen auf dem Western Blot aufgereinigter Viruspartikel eine Bande detektiert wurde, die dem Fusionsprotein aus pIX-Ova entsprach, und zum andern auch eine Inkubation der Virusproben – aktiv Diskussion 86 sowie inaktiv – mit dem Serum Adenovirus-immunisierter Mäuse ein positives Ergebnis im Dot Blot erbrachte, was für einen Erhalt der immundominaten Epitope spricht. Elektronenmikroskopische Aufnahmen einer anderen Arbeitsgruppe von unbehandelten und UV-behandelten Adenoviren untermauern dieses Ergebnis, da kein Unterschied zwischen den Viruspräparationen vorlag [180]. Auch die Aufnahmefähigkeit blieb durch die UV-Behandlung unbeeinträchtigt, da nach Infektion von HEK-293A Zellen mit aktivem und inaktivem Virus die gleiche Menge Ova-Protein intrazellulär nachgewiesen wurde. Die Spezifizität dieses Tests wurde durch die eingesetzten Kontrollen, lösliches Protein, welches nicht aufgenommen werden sollte, und ein anderes Virus, noch unterstrichen. Im nächsten Schritt sollte eine vergleichende Studie zeigen, inwieweit virale Partikel und Nanopartikel zu einer Aktivierung von DZ führen. Die Aufnahme von Nanopartikel von DZ wurde im Rahmen der vorliegenden Arbeit erfolgreich nachgewiesen. Mehrere Studien belegen zudem die Aufnahme von Adenoviren durch DZ, wobei diese mit einer hohen Infektionsdosis infiziert werden müssen. Die schlechte Infektiösität liegt dabei in der geringen Expression des CAR-Rezeptors bzw. dem Nichtvorhandensein von zellulären Integrinen begründet. Dennoch kommt es bei einer MOI von 1000 zu einer Infektionsrate von 96% [181], wobei bei diesen Zellen kein zytopathischer Effekt auftritt [181-184]. Bei der vergleichenden Untersuchung der Aktivierung von DZ durch Adenovirus und Nanopartikel waren aktive und UVinaktivierte Viren zu gleichen Teilen in der Lage, die Aktivierungsmarker CD80 und CD86 hoch zu regulieren. Dies ist konsistent mit der früheren Beobachtung einer Genexpression-unabhängigen Aktivierung, die auch mit UV-inaktiviertem Virus durchgeführt wurde [185]. In diesem Zusammenhang wurde zusätzlich eine Hochregulation weiterer Marker gezeigt, u. a. CD40 und MHC-II, auf die im Rahmen der vorliegenden Arbeit verzichtet wurde [181, 185]. Bei den Protein-beladenen Partikeln hingegen konnten nur die 220 sowie 340 nm Partikel DZ erfolgreich aktivieren. Dies steht teilweise im Widerspruch zu einer früheren Veröffentlichung, in der eine messbare Aktivierung von DZ durch Ova-beladene Nanopartikeln erst durch nachträgliche LPS-Stimulation erfolgte [178]. Zusätzlich zur Hochregulation bestimmter Marker kommt es nach Aktivierung zur Ausschüttung proinflammatorischer Zytokine [186]. Im Rahmen der vorliegenden Arbeit wurden die Typ-I-Interferone α und β erfasst. Beide wurden in großen Mengen von den Zellen ausgeschüttet, die mit Adenovirus infiziert waren. Wie auch bei dem Diskussion 87 Nachweis über FACS-Analyse war die Produktion bei inaktivem Virus genauso hoch wie bei aktivem, was nochmals eine Aktivierung der Zellen unabhängig von der Genexpression bestätigt und auch mit schon veröffentlichten Daten übereinstimmt [109]. Eine mögliche Erklärung bietet eine Aktivierung über den in den Endosomen lokalisierten Toll-like-Rezeptor 9, der dsDNA erkennt, dadurch die MyD88-Signalkaskade und somit die NFκB-vermittelte Aktivierung der IFN-Typ-I-Produktion in Gang setzt. Im Falle von Makrophagen tritt zudem das RGD-Motiv der Pentonbasis mit β3 Integrinen in Kontakt und vermittelt so die Poduktion bestimmter Zytokine und Chemokine. Möglicherweise ist dies auch bei DZ der Fall [187]. Zusätzlich konnte in DZ für replizierenden, nicht-replizierenden und UV-inaktivierten Adenovirus eine Expression von Il-6, sowie IL-12p40 nachgewiesen werden, auf deren Messung im Rahmen dieser Arbeit verzichtet wurde [188]. Ein Grund für die mangelnde Aktivierung der DZ durch Nanopartikel ist vermutlich das Fehlen eines kostimulatorischen Signals, da die Partikel selbst inert sind und keine Aktivierung hervorrufen. Dennoch waren die DZ in der Lage, das internalisierte Antigen zu prozessieren und über MHC-I-Komplexe an CD8+ T-Zellen zu präsentieren. Eine andere Arbeitsgruppe kam schon zuvor zu einem ähnlichen Ergebnis, auch in diesem Fall wurde ein in vitro Proliferationstest mit Ovalbumin-beladenen Nanopartikeln durchgeführt [178]. Anscheinend ist die Entlassung aus dem Endosom sowohl von Nanopartikeln als auch Adenoviren gewährleistet. Möglichweise ist jedoch der Endozytose-Mechanismus ein anderer und somit der intrazellulär zurückgelegte Weg. Um dies näher zu betrachten, wurden im Rahem der vorliegenden Arbeit verschiedene Endozytosewege gehemmt und der Einfluss auf die Aufnahme untersucht. Die Aufnahme von löslichem Ovalbumin ließ sich nicht hemmen. Die Aufnahme von Protein und löslichen Antigenen soll größtenteils über Makropinozytose erfolgen [189, 190], welche durch die hier verwendeten Hemmer nicht inhibiert wurde. Ein weiterer Endozytoseweg ist die Clathrin-vermittelte Aufnahme. Dabei lagern sich Chlathrinmoleküle auf der Innenseite der Membran an und krümmen diese, bis Invaginationen von etwa 150 nm entstehen. Diese Vesikelabschnürungen, die Clathrin-Körbchen genannt werden, werden über einen mechanochemisch durch Dynamin vermittelten Prozess abgeschnürt. Dynamin, eine GTPase, lagert sich dabei an den Vesikelhals an und schnürt diesen ab. Anschließend werden die Vesikel zu den Endosomen transportiert [191]. Adenoviren des Typs 2 und 5 sollen - wie auch kleinere Nanopartikel - über Clathrin-vermittelte Endozytose mit Involvierung des Adaptorproteins 2 aufgenommen werden [192]. Diskussion 88 Diese Daten konnten jedoch im Rahmen der vorliegenden Arbeit nur teilweise reproduziert werden, da Chloropromazin, ein Clathrin-Hemmer, zu gleichen Teilen die Aufnahme von 24 nm sowie 340 nm Partikeln inhibierte. Auch Genestein, ein Inhibitor des Caveolae-vermittelten Endozytoseweges, zeigte keine Wirkung. Caveolae, flaschenförmige Invaginationen der Plasmamembran, gehören zur Untergruppe der „Lipid rafts“ und enthalten als Charakteristikum Caveolin-1 [193-195]. Eine Hemmung der Aufnahme von 500 nm Partikeln durch Genestein ist jedoch beschrieben worden [171]. Möglicherweise liegen die Partikel mit 340 nm noch im Bereich „intermediärer“ Partikel, die andere Wege zur Internalisierung nutzen. Ein weiterer überraschender Befund war zudem, dass inaktives Virus trotz eingesetzter Hemmstoffe fast zu 100 % aufgenommen wurde. Auch kann ein Ausweichen auf andere Internalisierungswege eine mögliche Erklärung bieten. Für den Vergleich von löslichem Protein und Protein-beladenen Nanopartikeln hinsichtlich ihrer Immunogenität in vivo wurden drei verschiedene Proteinmengen gebunden auf 93 nm Partikeln sowie jeweils die analoge Menge an löslichem Ovalbumin intramuskulär appliziert. Lösliches Ovalbumin induzierte im Falle aller applizierten Proteinmengen signifikant niedrigere Antikörperantworten als die gleiche Menge auf Partikel gebunden. Dabei waren zwar 500 ng Ova auf Partikeln noch ausreichend, um nach einer einmaligen Immunisierung eine signifikante Antikörperantwort zu induzieren, 50 ng jedoch nicht mehr. Während lösliches Protein also kaum messbare Immunantworten induziert, kann durch die Immobilisierung auf PolystyrenPartikeln eine signifikante Erhöhung festgestellt werden. Mit einer Gesamtmenge von 5 µg Protein wurde eine gute Antikörperantwort induziert, so dass diese Menge beibehalten wurde, um die optimale Route für die Nanopartikelapplikation zu evaluieren. Die Untersuchung der Antikörper-vermittelten Immunantwort zur Ermittlung der besten Applikationsroute ergab im Rahmen der vorliegenden Arbeit eine Abhängigkeit von der Partikelgröße. Bei allen eingesetzen Größen fand sich eine gute humorale Immunantwort nach Applikation, wobei insbesondere die größeren Partikel zwischen 93 nm und 340 nm bei allen Applikationsrouten die beste Antwort lieferten. Dies könnte in Zusammenhang mit der Depotwirkung größerer Partikel stehen [196]. Nach Applikation blieb ein Teil der Partikel an der Injektionsstelle und lieferte so über einen langfristigen Zeitraum die Möglichkeit, von einwandernden Immunzellen erkannt bzw. aufgenommen zu werden. Dadurch scheint die erhöhte Präsentationsdauer für die Induktion von Antikörpern von Vorteil zu sein. Als beste Applikations- Diskussion 89 route stellten sich die plantare sowie intramuskuläre Injektion heraus, da so die höchste Antikörperantwort erreicht wurde. Auch für Adenoviren ist die plantare Injektion in die Hinterpfoten als die optimale Applikationsroute beschrieben [197]. Möglicherweise ist bedingt durch den hohen interstitiellen Druck in der Pfote eine höhere Transduktionseffizienz oder ein schnellerer Transport zu den nächstgelegenen Lymphknoten gegeben. Nach der Evaluation der Applikationsroute sollte im nächsten Schritt der Vergleich der durch Nanopartikel und virale Partikel induzierten Immunantwort bei gleicher Proteinmenge erfolgen. Da 1010 virale Partikel in vielen Immunisierungsstudien eingesetzt werden, sollte die Proteinmenge an Partikel gebunden daran angepasst werden. Eine Quantifizierung ergab eine Ovalbumin-Menge von 50 ng, die auf 1010 viralen Partikeln präsentiert wurde. Eine weitere Veränderung zu den vorhergehenden Versuchen stellte die Anwendung eines Prime-Boost-Immunisierungsschemas dar, wodurch nachweislich die Immunantwort gesteigert werden kann [198]. Aufgrund der Induktion einer zellulären Antwort wurden die 24 nm großen Partikel gewählt, die 93 nm großen Partikel spiegelten eine vergleichbare Größe zu den Adenoviren wieder und 340 nm große Partikel wurden aufgrund möglichweise anderer Aufnahme-, Prozessierungs- bzw. Immuninduktions-Mechanismen ausgewählt. Während kaum bzw. keine Antikörper in Form des Subtyps IgG2a, der bei einer TH1 Antwort gebildet wird, bei den drei Partikelgruppen 24POva, 93POva und 340POva induziert wurde, fanden sich stärkere Reaktionen bei AdVpIX-OvapIX-Ova bzw. auch bei AdVpIX-Ova immunisierten Tieren. Adenoviren können sowohl IgG2a als auch IgG1 induzieren und decken somit ein breites Spektrum ab [111]. Im Falle des Subtyps IgG1, welcher bei Einsetzen einer TH2 abhängigen Immuntwort gebildet wird, ließ sich zumindest nach der Auffrischungsimmunisierung bei 93POva ein signifikanter Anstieg feststellen. Dies steht im Einklang mit anderen Studien, bei denen auch eine Ausprägung der Immunantwort in Richtung TH2 auftrat [152]. Zwar scheint die Expression des Transgens sehr wichtig zu sein, um eine hohe Antikörperantwort zu bekommen, dennoch spricht die signifikante Induktion der Antikörpermenge bei inaktivem AdVpIX-Ova im Vergleich zum Serum naiver Tiere für eine Erkennung des Antigens auf der viralen Oberfläche und führt möglicherweise durch zusätzliche Erkennung immundominater Epitope des Kapsids zu einer Steigerung der Immunantwort. Somit scheint die Präsentation des Proteins auf dem Viruskapsids alleine Diskussion 90 eine gute Alternative zur Applikation von rekombinaten Proteinen zu sein oder zumindest im Fall viraler Vektoren einen zusätzlichen Vorteil neben der Expression zu bieten. Um den Beitrag der zellulären Komponente der Immunantwort bei Etablierung einer Antikörper-vermittelten humoralen Immunität zu bestimmen, wurde eine CD4+ T-Zell Depletion zum Zeitpunkt der Immunisierungen durchgeführt [199]. Erstaunlicherweise konnten bei keiner der Gruppen Antikörper des Typs IgG detektiert werden, was für eine T-Zell abhängige Aktivierung von B-Zellen spricht. Doch auch bei den adenoviralen Vektoren ließ sich kein signifikanter Anstieg der Antikörpermenge verzeichnen. Dies fand sich schon bei mehreren Untersuchungen. So fehlte eine Antikörperproduktion gegen adenovirale Proteine in Form von neutralisierenden Antikörpern nach α-CD4-Behandlung [200]. Möglichweise sind Antikörper des Subtyps IgM produziert worden, die vor allem durch T-Zell unabhängige Antigene induziert werden und bereits eine Woche nach Immunisierung nachweisbar sind. Auf die Bestimmung wurde jedoch im Rahmen der vorliegenden Arbeit verzichtet. Weitergehend scheinen CD4+ Zellen bei adenoviraler Applikation einen Einfluss auf die CD8+ Population zu nehmen, da im Falle des Depletionsversuchs eine größere Menge an Zytokin-produzierenden CD8+ T-Zellen festzustellen war, als dies im vorhergehenden Versuch – bei Einsatz der gleichen Menge sowie des gleichen Virusstocks - der Fall war. Möglichweise spielen in diesem Zusammenhang CD4+CD25+ T-Zellen, die als regulatorische T-Zellen (Treg) Einfluss auf das Immunsystem nehmen, eine Rolle, wie es bspw. bei einer DNA-Immunisierung gegen HBV der Fall war, wo Treg die Expansion Antigen-spezifischer CD8+ T-Zellen supprimierten [201]. Die Untersuchung der CD8+ T-Zellantwort der Tiere, die mit inaktivem AdVpIX-Ova immunisiert wurden, erbrachte in Fall der Depletions-Studie -- im Gegensatz zu der vergleichenden Studie ohne CD4-Depletion -- einen signifikant höheren Anteil INFγproduzierender CD8+ T-Zellen im Vergleich zu naiven Tieren. Scheinbar reichte der Einfluss der CD4+ T-Zellen bei der vergleichenden Studie ausreichend gewesen, um den Anteil an (INFγ+CD107a+)CD8+ T-Zellen soweit zu reduzieren, dass kein signifikanter Unterschied mehr zu den Zellen naiver Tiere festzustellen war. Da die induzierten T-Zell-Antworten jedoch insgesamt bei dem inaktiven Virus tendenziell höher waren als bei Nanopartikel-immunisierten Tieren, spricht für die adjuvante Wirkung des Kapsids. Insbesondere die IFNγ sezernierenden Zellen sind dabei erwünscht, da Diskussion 91 IFNγ ein Zytokin darstellt, welches für eine bevorzugte Induktion einer TH1 Differenzierung bekannt ist. TH1 Antworten sind insbesondere bei antiviralen Immunisierungen erwünscht [202, 203]. In geringem Maße ließ sich auch eine IL-4 Produktion feststellen, ein Zytokin, das von CD4+ T-Zellen produziert wird, um die B-ZellDifferenzierung zu beeinflussen [204]. Dieses größtenteils durch die Applikation von Nanopartikeln größer als 100 nm induziert [152]. Den mit Nanopartikel immunisierten Tieren fehlten hingegen sowohl Antikörper als auch Zytokin-produzierende CD8+ T-Zellen, obwohl im Falle des Depletionsversuches die 10fache Menge an Ovalbumin verwendet wurde, um mögliche Antikörperantworten besser detektieren zu können. Zudem zeigten die Ergebnisse, dass 50 ng Protein an Nanopartikel gebunden, unabhängig von deren Größe, für eine gute humorale und zelluläre Immunaktivierung nicht ausreichte. Dennoch ist nicht außer Acht zu lassen, dass bei Einsatz größerer Mengen an Protein (5 µg) ein messbares Level an immunmodulatorischen Komponenten produziert und ausgeschüttet wurde und dieses annähernd so hoch ist wie bei Immunisierung mit Adenoviren. Dies weist auf das Potential von nanopartikulären Strukturen zur Verbesserung Proteinbasierender Vakzinansätze hin. Dennoch scheint die klinische Relevanz fraglich, da die von anderen Arebitsgruppen hervorgehobene Depotwirkung der PolystyrenPartikel aufgrund deren Nicht-Abbaubarkeit eher als Nachteil ausgelegt werden sollte. Ein weiterer problematischer Aspekt ist, dass bei einem direkten Vergleich Transgen-exprimierender und UV-inaktivierter Adenoviren der exprimierende Vektor im Vorteil zu sein scheint. Dieser Vergleich ist jedoch schwierig, da es sich bei dem einen Ansatz um eine DNA-Vakzine, bei dem UV-inaktivierten Vektor jedoch um eine Proteinvakzine handelt. Da der Fokus bei Letzteren auf einer guten Immuninduktion mit möglichst wenig Proteineinsatz liegen sollte, scheinen im Niedrigdosis-Bereich UV-inaktivierte Nanopartikel eine weitaus vielversprechendere Alternative als beladene Nanopartikel aus Polystyren darzustellen, da sie sowohl zelluläre als auch humorale Komponenten aktivierten. Zusammenfassung 5 92 Zusammenfassung Die Immunisierung mit rekombinantem Protein löst in vielen Fällen nur geringe Immunreaktionen aus, die sich zumeist nur auf humorale Immunantworten beschränken. Aus diesem Grund sollten im Rahmen der vorliegenden Arbeit mit dem Modellantigen Ovalbumin beladene Polystyren-Nanopartikel und nicht-expri- mierende, adenovirale Vektoren, die Ovalbumin auf der Oberfläche präsentieren, näher auf ihre Immunogenität untersucht werden. • Die Nanopartikel ließen sich erfolgreich mit verschiedenen Proteinen beladen und es wurde in vitro eine Aufnahme durch Antigen-präsentierende Dendrititsche Zellen belegt. Diese prozessierten das Antigen und präsentierten es CD8+ TZellen. • Die UV-Inaktivierung von Adenoviren resultierte in dem Verlust ihrer Infektiösität, während das adenovirale Kapsid und die darauf präsentierten Proteine jedoch intakt blieben. • Die Produktion von Immunoglobulinen des Typs G nach Immunisierung mit Protein bzw. beladenen Nanopartikeln war dosisabhängig, wobei die AntikörperMenge bei Gabe von löslichem Protein signifikant niedriger war als bei der äquivalente Menge Protein auf 93 nm Partikel gebunden. • Die plantare Applikation von 5 µg Ova gebunden an Nanopartikel unterschiedlicher Größe stellte sich im murinen Modell im Vergleich zu intramuskulärer, intraperitonealer und subkutaner Applikation als die optimale Route heraus um hohe Antikörperantworten zu induzieren. Nur Partikel von 24 und 60 nm induzierten eine zelluläre Immunantwort und führten zu Zytokin-produzierenden CD8+ T-Zellen. • Bei gleicher Menge an Protein (50 ng) induzierten UV-inaktivierte Adenoviren mit Präsentation des Proteins auf ihrer Oberfläche höhere Antikörper und CD8+ sowie CD4+-Antworten als Ovalbumin-beladene Polystyren-Nanopartikel. • Die Antikörperantwort nach Immunisierung mit Adenoviren oder mit Protein beladenen Nanopartikeln war CD4+ T-Zell abhängig, bei adenoviral immunisierten Tieren wurde aber auch ohne CD4+ Zellen eine starke CD8+ T-Zell-Antwort induziert. Abstract 6 93 Abstract The immunization with recombinant protein often elicits only a moderate immune reaction, which is mainly restricted to humoral responses. Therefore, ovalbumincoated polystyrene-nanoparticles and adenoviral vectors presenting the antigen on their viral capsids were investigated for their immunogenicity. • Nanoparticles could be coated with different proteins. The uptake by antigenpresenting cells was shown in vitro. The cells processed the antigen and presented it to CD8+ T cells. • The UV-inactivation of adenoviruses resulted in the loss of infectivity, the adenoviral capsid and the exposed proteins on the viral surface remained intact. • The production of IgG antibodies after immunization with protein and coated nanoparticles, respectively, was dose-dependent. The antibody amount after protein immunization was significantly lower than after immunization with the equal amount of protein coated on 93 nm sized nanoparticles. • In comparison to intramuscular, intraperitoneal or subcutaneous application routes, footpad application turned out to be the optimal route in the murine model for the induction of high antibody responses after immunization with 5 µg ovalbumin coated on differently sized nanoparticles. Only particles of 24 nm and 60 nm induced a cellular immune reponse resulting in cytokine-producing CD8+ T cells. • Using the same amount of protein (50 ng), UV-inactivated adenovirus presenting the antigen on the surface induced higher antibody and CD8+ T cell as well as CD4+ T cell responses compared to ovalbumin-coated polystyrene-nanoparticles. • The antibody response after immunization with adenovirus and protein coated nanoparticles was CD4+ T cell dependent. However, the CD8+ response did not depend on the help of CD4+ T cells and elicited strong responses in mice immunized with viral vectors. Literatur 94 7 Literatur [1] Inaba K, Metlay JP, Crowley MT, Steinman RM (1990) Dendritic cells pulsed with protein antigens in vitro can prime antigen-specific, MHC-restricted T cells in situ. J Exp Med 172:631-40 [2] Banchereau J, Steinman RM (1998) Dendritic cells and the control of immunity. Nature 392:245-52 [3] Inaba K, Inaba M, Naito M, Steinman RM (1993) Dendritic cell progenitors phagocytose particulates, including Bacillus Calmette-Guerin organisms, and sensitize mice to mycobacterial antigens in vivo. J Exp Med 178:479-88 [4] Moll H, Fuchs H, Blank C, Röllinghoff M (1993) Langerhans cells transport Leishmania major from the infected skin to the draining lymph node for presentation to antigen-specific T cells. Eur J Immunol 23:1595-601 [5] Svensson M, Stockinger B, Wick MJ (1997) Bone marrow-derived dendritic cells can process bacteria for MHC-I and MHC-II presentation to T cells. J Immunol 158:4229-36 [6] Allavena P, Chieppa M, Monti P, Piemonti L (2004) From pattern recognition receptor to regulator of homeostasis: the double-faced macrophage mannose receptor. Crit Rev Immunol 24:179-92 [7] Jiang W, Swiggard WJ, Heufler C, Peng M, Mirza A, Steinman RM, Nussenzweig MC (1995) The receptor DEC-205 expressed by dendritic cells and thymic epithelial cells is involved in antigen processing. Nature 375:151-5 [8] Sallusto F, Lanzavecchia A (1994) Efficient presentation of soluble antigen by cultured human dendritic cells is maintained by granulocyte/macrophage colony-stimulating factor plus interleukin 4 and downregulated by tumor necrosis factor alpha. J Exp Med 179:1109-18 [9] Hawiger D, Inaba K, Dorsett Y, Guo M, Mahnke K, Rivera M, Ravetch JV, Steinman RM, Nussenzweig MC (2001) Dendritic cells induce peripheral T cell unresponsiveness under steady state conditions in vivo. J Exp Med 194:76979 [10] Bonifaz L, Bonnyay D, Mahnke K, Rivera M, Nussenzweig MC, Steinman RM (2002) Efficient targeting of protein antigen to the dendritic cell receptor DEC205 in the steady state leads to antigen presentation on major Literatur 95 histocompatibility complex class I products and peripheral CD8+ T cell tolerance. J Exp Med 196:1627-38 [11] Liu K, Iyoda T, Saternus M, Kimura Y, Inaba K, Steinman RM (2002) Immune tolerance after delivery of dying cells to dendritic cells in situ. J Exp Med 196:1091-7 [12] Romani N, Reider D, Heuer M, Ebner S, Kampgen E, Eibl B, Niederwieser D, Schuler G (1996) Generation of mature dendritic cells from human blood. An improved method with special regard to clinical applicability. J Immunol Methods 196:137-51 [13] Bender A, Sapp M, Schuler G, Steinman RM, Bhardwaj N (1996) Improved methods for the generation of dendritic cells from nonproliferating progenitors in human blood. J Immunol Methods 196:121-35 [14] Inaba K, Turley S, Iyoda T, Yamaide F, Shimoyama S, Reis e Sousa C, Germain RN, Mellman I, Steinman RM (2000) The formation of immunogenic major histocompatibility complex class II-peptide ligands in lysosomal compartments of dendritic cells is regulated by inflammatory stimuli. J Exp Med 191:927-36 [15] Granucci F, Vizzardelli C, Pavelka N, Feau S, Persico M, Virzi E, Rescigno M, Moro G, Ricciardi-Castagnoli P (2001) Inducible IL-2 production by dendritic cells revealed by global gene expression analysis. Nat Immunol 2:882-8 [16] Kitajima T, Ariizumi K, Bergstresser PR, Takashima A (1996) A novel mechanism of glucocorticoid-induced immune suppression: the inhibiton of T cell-mediated terminal maturation of a murine dendritic cell line. J Clin Invest 98:142-7 [17] Barratt-Boyes SM, Zimmer MI, Harshyne LA, Meyer EM, Watkins SC, Capuano S, Murphey-Corb M, Falo LD, Donnenberg AD (2000) Maturation and trafficking of monocyte-derived dendritic cells in monkeys: implications for dendritic cell-based vaccines. J Immunol 164:2487-95 [18] Kaisho T (2007) Elucidating the mechanism behind immunity using dendritic cells. Riken Res Frontl 2:1 [19] Falo LD, Kovacsovics-Bankowski M, Thompson K, Rock KL (1995) Targeting antigen into the phagocytic pathway in vivo induces protective tumor immunity. Nat Med 1:649-53 Literatur [20] 96 Staerz UD, Karasuyama H, Garner AM (1987) Cytotoxic T lymphocytes against a soluble protein. Nature 329:449-51 [21] Udono H, Srivastava PK (1993) Heat shock protein 70-associated peptides elicit specific cancer immunity. J Exp Med 178:1391-6 [22] Kapsenberg ML (2003) Dendritic-cell control of pathogen-driven T-cell polarization. Nat Rev Immunol 3:984-93 [23] O'Garra A (1998) Cytokines induce the development of functionally heterogeneous T helper cell subsets. Immunity 8:275-83 [24] Heufler C, Koch F, Stanzl U, Topar G, Wysocka M, Trinchieri G, Enk A, Steinman RM, Romani N, Schuler G (1996) Interleukin-12 is produced by dendritic cells and mediates T helper 1 development as well as interferongamma production by T helper 1 cells. Eur J Immunol 26:659-68 [25] Macatonia SE, Hosken NA, Litton M, Vieira P, Hsieh CS, Culpepper JA, Wysocka M, Trinchieri G, Murphy KM, O'Garra A (1995) Dendritic cells produce IL-12 and direct the development of Th1 cells from naive CD4+ T cells. J Immunol 154:5071-9 [26] Janeway CA (2002) Immunologie. Heidelberg: Spektrum Verlag [27] Sallusto F, Lanzavecchia A, Arakaki M, Ahmed R (2010) From vaccines to memory and back. Immunity 33:451-63 [28] Paul WE, Zhu J (2010) How are TH2-type immune responses initiated and amplified? Nat Rev Immunol 10:225-35 [29] Bonilla FA, Oettgen HC (2010) Adaptive immunity. J Allergy Clin Immunol 125:33-40 [30] Lemckert AA, Goudsmit J, Barouch DH (2004) Challenges in the search for an HIV vaccine. Eur J Epidemiol 19:513-6 [31] Marthas ML, Miller CJ, Sutjipto S, Higgins J, Torten J, Lohman BL, Unger RE, Ramos RA, Kiyono H, McGhee JR (1992) Efficacy of live-attenuated and whole-inactivated simian immunodeficiency virus vaccines against vaginal challenge with virulent SIV. J Med Primatol 21:99-107 [32] Whitney JB, Ruprecht RM (2004) Live attenuated HIV vaccines: pitfalls and prospects. Curr Opin Infect Dis 17:17-26 [33] Dubensky TW, Campbell BA, Villarreal LP (1984) Direct transfection of viral and plasmid DNA into the liver or spleen of mice. Proc Natl Acad Sci U S A 81:7529-33 Literatur [34] 97 Wolff JA, Malone RW, Williams P, Chong W, Acsadi G, Jani A, Felgner PL (1990) Direct gene transfer into mouse muscle in vivo. Science 247:1465-8 [35] Wolff JA, Ludtke JJ, Acsadi G, Williams P, Jani A (1992) Long-term persistence of plasmid DNA and foreign gene expression in mouse muscle. Hum Mol Genet 1:363-9 [36] Mayordomo JI, Zorina T, Storkus WJ, Zitvogel L, Celluzzi C, Falo LD, Melief CJ, Ildstad ST, Kast WM, Deleo AB (1995) Bone marrow-derived dendritic cells pulsed with synthetic tumour peptides elicit protective and therapeutic antitumour immunity. Nat Med 1:1297-302 [37] Harding CV, Song R (1994) Phagocytic processing of exogenous particulate antigens by macrophages for presentation by class I MHC molecules. J Immunol 153:4925-33 [38] Schwarz TF (2009) Clinical update of the AS04-adjuvanted human papillomavirus-16/18 cervical cancer vaccine, Cervarix. Adv Ther 26:983-98 [39] Fries LF, Dillon SB, Hildreth JE, Karron RA, Funkhouser AW, Friedman CJ, Jones CS, Culleton VG, Clements ML (1993) Safety and immunogenicity of a recombinant protein influenza A vaccine in adult human volunteers and protective efficacy against wild-type H1N1 virus challenge. J Infect Dis 167:593-601 [40] Ichinohe T, Watanabe I, Ito S, Fujii H, Moriyama M, Tamura S, Takahashi H, Sawa H, Chiba J, Kurata T, Sata T, Hasegawa H (2005) Synthetic doublestranded RNA poly(I:C) combined with mucosal vaccine protects against influenza virus infection. J Virol 79:2910-9 [41] Llopiz D, Dotor J, Zabaleta A, Lasarte JJ, Prieto J, Borras-Cuesta F, Sarobe P (2008) Combined immunization with adjuvant molecules poly(I:C) and antiCD40 plus a tumor antigen has potent prophylactic and therapeutic antitumor effects. Cancer Immunol Immunother 57:19-29 [42] Zabaleta A, Arribillaga L, Llopiz D, Dotor J, Lasarte JJ, Prieto J, Borras-Cuesta F, Esteban JI, Quer J, Vayreda F, Sarobe P (2007) Induction of potent and long-lasting CD4 and CD8 T-cell responses against hepatitis C virus by immunization with viral antigens plus poly(I:C) and anti-CD40. Antiviral Res 74:25-35 [43] Cong Y, Jupelli M, Guentzel MN, Zhong G, Murthy AK, Arulanandam BP (2007) Intranasal immunization with chlamydial protease-like activity factor Literatur 98 and CpG deoxynucleotides enhances protective immunity against genital Chlamydia muridarum infection. Vaccine 25:3773-80 [44] Klinman DM (2006) Adjuvant activity of CpG oligodeoxynucleotides. Int Rev Immunol 25:135-54 [45] Zimmermann S, Dalpke A, Heeg K (2008) CpG oligonucleotides as adjuvant in therapeutic vaccines against parasitic infections. Int J Med Microbiol 298:3944 [46] Dela Cruz JS, Lau SY, Ramirez EM, De Giovanni C, Forni G, Morrison SL, Penichet ML (2003) Protein vaccination with the HER2/neu extracellular domain plus anti-HER2/neu antibody-cytokine fusion proteins induces a protective anti-HER2/neu immune response in mice. Vaccine 21:1317-26 [47] Nayak BP, Sailaja G, Jabbar AM (2003) Enhancement of gp120-specific immune responses by genetic vaccination with the human immunodeficiency virus type 1 envelope gene fused to the gene coding for soluble CTLA4. J Virol 77:10850-61 [48] Tacken PJ, de Vries IJ, Gijzen K, Joosten B, Wu D, Rother RP, Faas SJ, Punt CJ, Torensma R, Adema GJ, Figdor CG (2005) Effective induction of naive and recall T-cell responses by targeting antigen to human dendritic cells via a humanized anti-DC-SIGN antibody. Blood 106:1278-85 [49] Ruzek MC, Kavanagh BF, Scaria A, Richards SM, Garman RD (2002) Adenoviral vectors stimulate murine natural killer cell responses and demonstrate antitumor activities in the absence of transgene expression. Mol Ther 5:115-24 [50] Shiver JW, Fu TM, Chen L, Casimiro DR, Davies ME, Evans RK, Zhang ZQ, Simon AJ, Trigona WL, Dubey SA, Huang L, Harris VA, Long RS, Liang X, Handt L, Schleif WA, Zhu L, Freed DC, Persaud NV, Guan L, Punt KS, Tang A, Chen M, Wilson KA, Collins KB, Heidecker GJ, Fernandez VR, Perry HC, Joyce JG, Grimm KM, Cook JC, Keller PM, Kresock DS, Mach H, Troutman RD, Isopi LA, Williams DM, Xu Z, Bohannon KE, Volkin DB, Montefiori DC, Miura A, Krivulka GR, Lifton MA, Kuroda MJ, Schmitz JE, Letvin NL, Caulfield MJ, Bett AJ, Youil R, Kaslow DC, Emini EA (2002) Replication-incompetent adenoviral vaccine vector immunity. Nature 415:331-5 elicits effective anti-immunodeficiency-virus Literatur [51] 99 Robinson HL, Amara RR (2005) T cell vaccines for microbial infections. Nat Med 11:S25-32 [52] Rowe WP, Huebner RJ, Gilmore LK, Parrott RH, Ward TG (1953) Isolation of a cytopathogenic agent from human adenoids undergoing spontaneous degeneration in tissue culture. Proc Soc Exp Biol Med 84:570-3 [53] Buchen-Osmond C (1997) Further progress in ICTVdB, a universal virus database. Arch Virol 142:1734-9 [54] Russell WC (2009) Adenoviruses: update on structure and function. J Gen Virol 90:1-20 [55] Monto AS (1992) Acute respiratory infections. Norwalk: Appleton and Lange [56] Stewart PL, Burnett RM, Cyrklaff M, Fuller SD (1991) Image reconstruction reveals the complex molecular organization of adenovirus. Cell 67:145-54 [57] Rux JJ, Burnett RM (2004) Adenovirus structure. Hum Gene Ther 15:1167-76 [58] Burnett RM (1985) The structure of the adenovirus capsid. II. The packing symmetry of hexon and its implications for viral architecture. J Mol Biol 185:125-43 [59] van Oostrum J, Burnett RM (1985) Molecular composition of the adenovirus type 2 virion. J Virol 56:439-48 [60] Pereira HG, Valentine RC, Russell WC (1968) Crystallization of an adenovirus protein (the hexon). Nature 219:946-7 [61] Benko M, Harrach B (2003) Molecular evolution of adenoviruses. Curr Top Microbiol Immunol 272:3-35 [62] Shortridge KF, Biddle F (1970) The proteins of adenovirus type 5. Arch Ges Virusforsch 29:1-24 [63] Bergelson JM (1999) Receptors mediating adenovirus attachment and internalization. Biochem Pharmacol 57:975-9 [64] Signas C, Akusjarvi G, Pettersson U (1985) Adenovirus 3 fiber polypeptide gene: implications for the structure of the fiber protein. J Virol 53:672-8 [65] Green NM, Wrigley NG, Russell WC, Martin SR, McLachlan AD (1983) Evidence for a repeating cross-beta sheet structure in the adenovirus fibre. EMBO J 2:1357-65 [66] Colby WW, Shenk T (1981) Adenovirus type 5 virions can be assembled in vivo in the absence of detectable polypeptide IX. J Virol 39:977-80 Literatur [67] 100 Meulenbroek RA, Sargent KL, Lunde J, Jasmin BJ, Parks RJ (2004) Use of adenovirus protein IX (pIX) to display large polypeptides on the viriongeneration of fluorescent virus through the incorporation of pIX-GFP. Mol Ther 9:617-24 [68] Furcinitti PS, van Oostrum J, Burnett RM (1989) Adenovirus polypeptide IX revealed as capsid cement by difference images from electron microscopy and crystallography. EMBO J 8:3563-70 [69] Parks RJ (2005) Adenovirus protein IX: a new look at an old protein. Mol Ther 11:19-25 [70] Li J, Fatima A, Komarova S, Ugai H, Uprety P, Roth JC, Wang M, Oster RA, Curiel DT, Matthews QL (2010) Evaluation of adenovirus capsid labeling versus transgene expression. Virol J 7:21 [71] Vellinga J, de Vrij J, Myhre S, Uil T, Martineau P, Lindholm L, Hoeben RC (2007) Efficient incorporation of a functional hyper-stable single-chain antibody fragment protein-IX fusion in the adenovirus capsid. Gene Ther 14:664-70 [72] Bayer W, Tenbusch M, Lietz R, Johrden L, Schimmer S, Überla K, Dittmer U, Wildner O (2010) Vaccination with an adenoviral vector that encodes and displays a retroviral antigen induces improved neutralizing antibody and CD4+ T-cell responses and confers enhanced protection. J Virol 84:1967-76 [73] He TC, Zhou S, da Costa LT, Yu L, Kinzler KW, Vogelstein B (1998) A simplified system for generating recombinant adenoviruses. Proc Natl Acad Sci U S A 95:2509-14 [74] Wilson JM (1996) Adenoviruses as gene-delivery vehicles. N Engl J Med 334:1185-7 [75] Danthinne X, Imperiale MJ (2000) Production of first generation adenovirus vectors: a review. Gene Ther 7:1707-14 [76] Kay MA, Glorioso JC, Naldini L (2001) Viral vectors for gene therapy: the art of turning infectious agents into vehicles of therapeutics. Nat Med 7:33-40 [77] Parks RJ, Chen L, Anton M, Sankar U, Rudnicki MA, Graham FL (1996) A helper-dependent adenovirus vector system: removal of helper virus by Cremediated excision of the viral packaging signal. Proc Natl Acad Sci U S A 93:13565-70 Literatur [78] 101 Yang Y, Li Q, Ertl HC, Wilson JM (1995) Cellular and humoral immune responses to viral antigens create barriers to lung-directed gene therapy with recombinant adenoviruses. J Virol 69:2004-15 [79] Russell WC (2000) Update on adenovirus and its vectors. J Gen Virol 81:2573-604 [80] Kochanek S, Clemens PR, Mitani K, Chen HH, Chan S, Caskey CT (1996) A new adenoviral vector: Replacement of all viral coding sequences with 28 kb of DNA independently expressing both full-length dystrophin and betagalactosidase. Proc Natl Acad Sci U S A 93:5731-6 [81] Hoffmann D, Meyer B, Wildner O (2007) Improved glioblastoma treatment with Ad5/35 fiber chimeric conditionally replicating adenoviruses. J Gene Med 9:764-78 [82] Gao W, Soloff AC, Lu X, Montecalvo A, Nguyen DC, Matsuoka Y, Robbins PD, Swayne DE, Donis RO, Katz JM, Barratt-Boyes SM, Gambotto A (2006) Protection of mice and poultry from lethal H5N1 avian influenza virus through adenovirus-based immunization. J Virol 80:1959-64 [83] Sullivan NJ, Geisbert TW, Geisbert JB, Shedlock DJ, Xu L, Lamoreaux L, Custers JH, Popernack PM, Yang ZY, Pau MG, Roederer M, Koup RA, Goudsmit J, Jahrling PB, Nabel GJ (2006) Immune protection of nonhuman primates against Ebola virus with single low-dose adenovirus vectors encoding modified GPs. PLoS Med 3:e177 [84] Santosuosso M, McCormick S, Zhang X, Zganiacz A, Xing Z (2006) Intranasal boosting with an adenovirus-vectored vaccine markedly enhances protection by parenteral Mycobacterium bovis BCG immunization against pulmonary tuberculosis. Infect Immun 74:4634-43 [85] Douglas JT (2007) Adenoviral vectors for gene therapy. Mol Biotechnol 36:7180 [86] Vanniasinkam T, Ertl HC (2005) Adenoviral gene delivery for HIV-1 vaccination. Curr Gene Ther 5:203-12 [87] Sumida SM, Truitt DM, Lemckert AA, Vogels R, Custers JH, Addo MM, Lockman S, Peter T, Peyerl FW, Kishko MG, Jackson SS, Gorgone DA, Lifton MA, Essex M, Walker BD, Goudsmit J, Havenga MJ, Barouch DH (2005) Neutralizing antibodies to adenovirus serotype 5 vaccine vectors are directed primarily against the adenovirus hexon protein. J Immunol 174:7179-85 Literatur [88] 102 Barouch DH, Pau MG, Custers JH, Koudstaal W, Kostense S, Havenga MJ, Truitt DM, Sumida SM, Kishko MG, Arthur JC, Korioth-Schmitz B, Newberg MH, Gorgone DA, Lifton MA, Panicali DL, Nabel GJ, Letvin NL, Goudsmit J (2004) Immunogenicity of recombinant adenovirus serotype 35 vaccine in the presence of pre-existing anti-Ad5 immunity. J Immunol 172:6290-7 [89] Roberts DM, Nanda A, Havenga MJ, Abbink P, Lynch DM, Ewald BA, Liu J, Thorner AR, Swanson PE, Gorgone DA, Lifton MA, Lemckert AA, Holterman L, Chen B, Dilraj A, Carville A, Mansfield KG, Goudsmit J, Barouch DH (2006) Hexon-chimaeric adenovirus serotype 5 vectors circumvent pre-existing antivector immunity. Nature 441:239-43 [90] Molinier-Frenkel V, Lengagne R, Gaden F, Hong SS, Choppin J, GaherySegard H, Boulanger P, Guillet JG (2002) Adenovirus hexon protein is a potent adjuvant for activation of a cellular immune response. J Virol 76:127-35 [91] Yang Y, Jooss KU, Su Q, Ertl HC, Wilson JM (1996) Immune responses to viral antigens versus transgene product in the elimination of recombinant adenovirus-infected hepatocytes in vivo. Gene Ther 3:137-44 [92] Dai Y, Schwarz EM, Gu D, Zhang WW, Sarvetnick N, Verma IM (1995) Cellular and humoral immune responses to adenoviral vectors containing factor IX gene: tolerization of factor IX and vector antigens allows for long-term expression. Proc Natl Acad Sci U S A 92:1401-5 [93] Yang Y, Greenough K, Wilson JM (1996) Transient immune blockade prevents formation of neutralizing antibody to recombinant adenovirus and allows repeated gene transfer to mouse liver. Gene Ther 3:412-20 [94] Buchbinder SP, Mehrotra DV, Duerr A, Fitzgerald DW, Mogg R, Li D, Gilbert PB, Lama JR, Marmor M, Del Rio C, McElrath MJ, Casimiro DR, Gottesdiener KM, Chodakewitz JA, Corey L, Robertson MN (2008) Efficacy assessment of a cell-mediated immunity HIV-1 vaccine (the Step Study): a double-blind, randomised, placebo-controlled, test-of-concept trial. Lancet 372:1881-93 [95] Holterman L, Vogels R, van der Vlugt R, Sieuwerts M, Grimbergen J, Kaspers J, Geelen E, van der Helm E, Lemckert A, Gillissen G, Verhaagh S, Custers J, Zuijdgeest D, Berkhout B, Bakker M, Quax P, Goudsmit J, Havenga M (2004) Novel replication-incompetent vector derived from adenovirus type 11 (Ad11) for vaccination and gene therapy: low seroprevalence and non-cross-reactivity with Ad5. J Virol 78:13207-15 Literatur [96] 103 Kostense S, Koudstaal W, Sprangers M, Weverling GJ, Penders G, Helmus N, Vogels R, Bakker M, Berkhout B, Havenga M, Goudsmit J (2004) Adenovirus types 5 and 35 seroprevalence in AIDS risk groups supports type 35 as a vaccine vector. AIDS 18:1213-6 [97] Lemckert AA, Grimbergen J, Smits S, Hartkoorn E, Holterman L, Berkhout B, Barouch DH, Vogels R, Quax P, Goudsmit J, Havenga MJ (2006) Generation of a novel replication-incompetent adenoviral vector derived from human adenovirus type 49: manufacture on PER.C6 cells, tropism and immunogenicity. J Gen Virol 87:2891-9 [98] Harrod KS, Hermiston TW, Trapnell BC, Wold WS, Whitsett JA (1998) Lungspecific expression of adenovirus E3-14.7K in transgenic mice attenuates adenoviral vector-mediated lung inflammation and enhances transgene expression. Hum Gene Ther 9:1885-98 [99] Lemckert AA, Sumida SM, Holterman L, Vogels R, Truitt DM, Lynch DM, Nanda A, Ewald BA, Gorgone DA, Lifton MA, Goudsmit J, Havenga MJ, Barouch DH (2005) Immunogenicity of heterologous prime-boost regimens involving recombinant adenovirus serotype 11 (Ad11) and Ad35 vaccine vectors in the presence of anti-ad5 immunity. J Virol 79:9694-701 [100] Thorner AR, Lemckert AA, Goudsmit J, Lynch DM, Ewald BA, Denholtz M, Havenga MJ, Barouch DH (2006) Immunogenicity of heterologous recombinant adenovirus prime-boost vaccine regimens is enhanced by circumventing vector cross-reactivity. J Virol 80:12009-16 [101] McCoy RD, Davidson BL, Roessler BJ, Huffnagle GB, Janich SL, Laing TJ, Simon RH (1995) Pulmonary inflammation induced by incomplete or inactivated adenoviral particles. Hum Gene Ther 6:1553-60 [102] Jooss K, Ertl HC, Wilson JM (1998) Cytotoxic T-lymphocyte target proteins and their major histocompatibility complex class I restriction in response to adenovirus vectors delivered to mouse liver. J Virol 72:2945-54 [103] Worgall S, Leopold PL, Wolff G, Ferris B, Van Roijen N, Crystal RG (1997) Role of alveolar macrophages in rapid elimination of adenovirus vectors administered to the epithelial surface of the respiratory tract. Hum Gene Ther 8:1675-84 [104] Berclaz PY, Zsengeller Z, Shibata Y, Otake K, Strasbaugh S, Whitsett JA, Trapnell BC (2002) Endocytic internalization of adenovirus, nonspecific Literatur 104 phagocytosis, and cytoskeletal organization are coordinately regulated in alveolar macrophages by GM-CSF and PU.1. J Immunol 169:6332-42 [105] Stilwell JL, McCarty DM, Negishi A, Superfine R, Samulski RJ (2003) Development and characterization of novel empty adenovirus capsids and their impact on cellular gene expression. J Virol 77:12881-5 [106] Kafri T, Morgan D, Krahl T, Sarvetnick N, Sherman L, Verma I (1998) Cellular immune response to adenoviral vector infected cells does not require de novo viral gene expression: implications for gene therapy. Proc Natl Acad Sci U S A 95:11377-82 [107] Taniguchi M, Seino K, Nakayama T (2003) The NKT cell system: bridging innate and acquired immunity. Nat Immunol 4:1164-5 [108] Benihoud K, Saggio I, Opolon P, Salone B, Amiot F, Connault E, Chianale C, Dautry F, Yeh P, Perricaudet M (1998) Efficient, repeated adenovirusmediated gene transfer in mice lacking both tumor necrosis factor alpha and lymphotoxin alpha. J Virol 72:9514-25 [109] Zhu J, Huang X, Yang Y (2007) Innate immune response to adenoviral vectors is mediated by both Toll-like receptor-dependent and -independent pathways. J Virol 81:3170-80 [110] Rhee EG, Blattmann JN, Kasturi SP, Kelley RP, Kaufman DR, Lynch DM, La Porte A, Simmons NL, Clark SL, Pulendran B, Greenberg PD, Barouch DH (2011) Multiple innate immune pathways contribute to the immunogenicity of recombinant adenovirus vaccine vectors. J Virol 85:315-23 [111] Gahery-Segard H, Juillard V, Gaston J, Lengagne R, Pavirani A, Boulanger P, Guillet JG (1997) Humoral immune response to the capsid components of recombinant adenoviruses: routes of immunization modulate virus-induced Ig subclass shifts. Eur J Immunol 27:653-9 [112] Kreuter J, Alyautdin RN, Kharkevich DA, Ivanov AA (1995) Passage of peptides through the blood-brain barrier with colloidal polymer particles (nanoparticles). Brain Res 674:171-4 [113] Sugimura T, Suzuki T, Chatchawanchonteera A, Sinuwonkwat P, Tsuda T, Murakami Y (2000) Application of latex beads agglutination test for the detection of the antibody against virus-infection-associated (VIA) antigen of foot-and-mouth disease (FMD) virus. J Vet Med Sci 62:805-7 Literatur 105 [114] Zolnik BS, Gonzalez-Fernandez A, Sadrieh N, Dobrovolskaia MA (2010) Nanoparticles and the immune system. Endocrinology 151:458-65 [115] Hall JB, dobrovolskaia MA, Parti AK, McNeil SE (2007) Characterization of nanoparticles for therapeutics. Nanomedicine 2:789-803 [116] Morein B, Sundquist B, Hoglund S, Dalsgaard K, Osterhaus A (1984) Iscom, a novel structure for antigenic presentation of membrane proteins from enveloped viruses. Nature 308:457-60 [117] Hu KF, Lovgren-Bengtsson K, Morein B (2001) Immunostimulating complexes (ISCOMs) for nasal vaccination. Adv Drug Deliv Rev 51:149-59 [118] Ozel M, Hoglund S, Gelderblom HR, Morein B (1989) Quaternary structure of the immunostimulating complex (Iscom). J Ultrastruct Mol Struct Res 102:2408 [119] Scheerlinck JP, Greenwood DL (2008) Virus-sized vaccine delivery systems. Drug Discov Today 13:882-7 [120] Morein F, Bengtsson KL (1998) Functional aspects of Iscoms. Immunol Cell Biol 76:295-9 [121] Sun HX, Xie Y, Ye YP (2009) ISCOMs and ISCOMATRIX. Vaccine 27:4388401 [122] Matrin A (1993) Physical pharmacy: physical chemical principles in the pharmaceutical sciences. Philadelphia: Lippincott Williams & Wilkins [123] Bouchemal K, Briancon S, Perrier E, Fessi H (2004) Nano-emulsion formulation using spontaneous emulsification: solvent, oil and surfactant optimisation. Int J Pharm 280:241-51 [124] Izquierdo P, Esquena J, Tadros TF, Dederen JC, Feng J, Garcia-Celma MJ, Azemar N, Solans C (2004) Phase behavior and nano-emulsion formation by the phase inversion temperature method. Langmuir 20:6594-8 [125] Zhou WY, Wang M, Cheung WL, Guo BC, Jia DM (2008) Synthesis of carbonated hydroxyapatite nanospheres through nanoemulsion. J Mater Sci Mater Med 19:103-10 [126] Makidon PE, Bielinska AU, Nigavekar SS, Janczak KW, Knowlton J, Scott AJ, Mank N, Cao Z, Rathinavelu S, Beer MR, Wilkinson JE, Blanco LP, Landers JJ, Baker JR (2008) Pre-clinical evaluation of a novel nanoemulsion-based hepatitis B mucosal vaccine. PLoS One 3:e2954 Literatur 106 [127] Cheng Y, Xu Z, Ma M, Xu T (2008) Dendrimers as drug carriers: applications in different routes of drug administration. J Pharm Sci 97:123-43 [128] Tomalia D, Dewald J, Hall M, Martin S, Smith P (1984) Dendrimers. 1st SPSJ International Polymer Conference; Kyoto. p. 65 [129] Trikalitis PN, Rangan KK, Bakas T, Kanatzidis MG (2001) Varied pore organization in mesostructured semiconductors based on the [SnSe4](4-) anion. Nature 410:671-5 [130] Corma A, Atienzar P, Garcia H, Chane-Ching JY (2004) Hierarchically mesostructured doped CeO2 with potential for solar-cell use. Nat Mater 3:3947 [131] Grosso D, Boissiere C, Smarsly B, Brezesinski T, Pinna N, Albouy PA, Amenitsch H, Antonietti M, Sanchez C (2004) Periodically ordered nanoscale islands and mesoporous films composed of nanocrystalline multimetallic oxides. Nat Mater 3:787-92 [132] Armatas GS, Kanatzidis MG (2006) Mesostructured germanium with cubic pore symmetry. Nature 441:1122-5 [133] Sun D, Riley AE, Cadby AJ, Richman EK, Korlann SD, Tolbert SH (2006) Hexagonal nanoporous germanium through surfactant-driven self-assembly of Zintl clusters. Nature 441:1126-30 [134] Faraji AH, Wipf P (2009) Nanoparticles in cellular drug delivery. Bioorg Med Chem 17:2950-62 [135] Yu WW (2008) Semiconductor quantum dots: synthesis and watersolubilization for biomedical applications. Expert Opin Biol Ther 8:1571-81 [136] Mozafari MR (2005) Liposomes: an overview of manufacturing techniques. Cell Mol Biol Lett 10:711-9 [137] Mozafari MR, Johnson C, Hatziantoniou S, Demetzos C (2008) Nanoliposomes and their applications in food nanotechnology. J Liposome Res 18:309-27 [138] Rytting E, Nguyen J, Wang X, Kissel T (2008) Biodegradable polymeric nanocarriers for pulmonary drug delivery. Expert Opin Drug Deliv 5:629-39 [139] Luppi B, Bigucci F, Cerchiara T, Zecchi V (2010) Chitosan-based hydrogels for nasal drug delivery: from inserts to nanoparticles. Expert Opin Drug Deliv 7:811-28 Literatur 107 [140] Lu JM, Wang X, Marin-Muller C, Wang H, Lin PH, Yao Q, Chen C (2009) Current advances in research and clinical applications of PLGA-based nanotechnology. Expert Rev Mol Diagn 9:325-41 [141] Athanasiou KA, Niederauer GG, Agrawal CM (1996) Sterilization, toxicity, biocompatibility and clinical applications of polylactic acid/polyglycolic acid copolymers. Biomaterials 17:93-102 [142] Dlugi AM, Miller JD, Knittle J (1990) Lupron depot (leuprolide acetate for depot suspension) in the treatment of endometriosis: a randomized, placebocontrolled, double-blind study. Lupron Study Group. Fertil Steril 54:419-27 [143] Ramqvist T, Andreasson K, Dalianis T (2007) Vaccination, immune and gene therapy based on virus-like particles against viral infections and cancer. Expert Opin Biol Ther 7:997-1007 [144] Villa LL, Costa RL, Petta CA, Andrade RP, Ault KA, Giuliano AR, Wheeler CM, Koutsky LA, Malm C, Lehtinen M, Skjeldestad FE, Olsson SE, Steinwall M, Brown DR, Kurman RJ, Ronnett BM, Stoler MH, Ferenczy A, Harper DM, Tamms GM, Yu J, Lupinacci L, Railkar R, Taddeo FJ, Jansen KU, Esser MT, Sings HL, Saah AJ, Barr E (2005) Prophylactic quadrivalent human papillomavirus (types 6, 11, 16, and 18) L1 virus-like particle vaccine in young women: a randomised double-blind placebo-controlled multicentre phase II efficacy trial. Lancet Oncol 6:271-8 [145] Jennings GT, Bachmann MF (2009) Immunodrugs: therapeutic VLP-based vaccines for chronic diseases. Annu Rev Pharmacol Toxicol 49:303-26 [146] Ludwig C, Wagner R (2007) Virus-like particles-universal molecular toolboxes. Curr Opin Biotechnol 18:537-45 [147] Skountzou I, Quan FS, Gangadhara S, Ye L, Vzorov A, Selvaraj P, Jacob J, Compans RW, Kang SM (2007) Incorporation of glycosylphosphatidylinositolanchored granulocyte-macrophage colony-stimulating factor or CD40 ligand enhances immunogenicity of chimeric simian immunodeficiency virus-like particles. J Virol 81:1083-94 [148] Reddy ST, van der Vlies AJ, Simeoni E, Angeli V, Randolph GJ, O'Neil CP, Lee LK, Swartz MA, Hubbell JA (2007) Exploiting lymphatic transport and complement activation in nanoparticle vaccines. Nat Biotechnol 25:1159-64 Literatur 108 [149] Ishihara T, Kubota T, Choi T, Higaki M (2009) Treatment of experimental arthritis with stealth-type polymeric nanoparticles encapsulating betamethasone phosphate. J Pharmacol Exp Ther 329:412-7 [150] Basarkar A, Singh J (2009) Poly (lactide-co-glycolide)-polymethacrylate nanoparticles for intramuscular delivery of plasmid encoding interleukin-10 to prevent autoimmune diabetes in mice. Pharm Res 26:72-81 [151] Thiele L, Rothen-Rutishauser B, Jilek S, Wunderli-Allenspach H, Merkle HP, Walter E (2001) Evaluation of particle uptake in human blood monocytederived cells in vitro. Does phagocytosis activity of dendritic cells measure up with macrophages? J Control Release 76:59-71 [152] Mottram PL, Leong D, Crimeen-Irwin B, Gloster S, Xiang SD, Meanger J, Ghildyal R, Vardaxis N, Plebanski M (2007) Type 1 and 2 immunity following vaccination is influenced by nanoparticle size: formulation of a model vaccine for respiratory syncytial virus. Mol Pharm 4:73-84 [153] Lindl T, Bauer J (1994) Zellkultur und Gewebekultur. Stuttgart: Gustav Fischer Verlag [154] Saiki RK, Gelfand DH, Stoffel S, Scharf SJ, Higuchi R, Horn GT, Mullis KB, Erlich HA (1988) Primer-directed enzymatic amplification of DNA with a thermostable DNA polymerase. Science 239:487-91 [155] Dieffenbach CW, Lowe TM, Dveksler GS (1993) General concepts for PCR primer design. PCR Methods Appl 3:30-7 [156] Marchuk D, Drumm M, Saulino A, Collins FS (1991) Construction of T-vectors, a rapid and general system for direct cloning of unmodified PCR products. Nucleic Acids Res 19:1154 [157] Trower MK, Elgar GS (1996) Cloning PCR products using T-vectors. Methods Mol Biol 58:313-24 [158] Sambrook J, Fritsch EF (1989) Molecular cloning - A laboratory manual. New York: Cold Spring Harbour Laboratory Press [159] Seyffert W, Gassen HG (1998) Lehrbuch der Genetik. Stuttgart: Gustav Fischer Verlag [160] Short JM, Fernandez JM, Sorge JA, Huse WD (1998) Lambda ZAP: a bacteriophage lambda expression vector with in vivo excision properties. Nucl Acid Res 16:7583-600 Literatur 109 [161] Miller IL, Palmer CD, Landman OE (1972) Comparison of deoxyribonucleic acid uptake and marker integration in bacilli and protoplasts of Bacillus subtilis. J Bacteriol 110:661-6 [162] Cohen SN, Chang AC, Hsu L (1972) Nonchromosomal antibiotic resistence in bacteria: genetic transformation of Escherichia coli by R-factor DNA. Proc Natl Acad Sci U S A 62:2110-4 [163] Davies J, Jacob F (1968) Genetic mapping of the regulator and operator genes of the lac operon. J Mol Biol 36:413-7 [164] Eckhard B (2001) Mikrobiologische Methoden: Eine Einführung in grundlegende Arbeitstechniken. Heidelberg: Spektrum Verlag [165] Schrimpf G (2002) Gentechnische Methoden: Eine Sammlung von Arbeitsanleitungen für das molekularbiologische Labor. Heidelberg: Spektrum Verlag [166] Laemmli UK (1970) Cleavage of structural proteins during the assembly of the head of bacteriophage T4. Nature 227:680-5 [167] Cotten M, Wagner E, Zatloukal K, Phillips S, Curiel DT, Birnstiel ML (1992) High-efficiency receptor-mediated delivery of small and large (48 kilobase gene constructs using the endosome-disruption activity of defective or chemically inactivated adenovirus particles. Proc Natl Acad Sci U S A 89:6094-8 [168] Cotten M, Saltik M, Kursa M, Wagner E, Maass G, Birnstiel ML (1994) Psoralen treatment of adenovirus particles eliminates virus replication and transcription while maintaining the endosomolytic activity of the virus capsid. Virology 205:254-61 [169] Hirschowitz EA, Weaver JD, Hidalgo GE, Doherty DE (2000) Murine dendritic cells infected with adenovirus vectors show signs of activation. Gene Ther 7:1112-20 [170] Parish CR, Warren HS (2002) Use of the intracellular fluorescent dye CFSE to monitor lymphocyte migration and proliferation. Curr Protoc Immunol Chapter 4:Unit 4 9 [171] Rejman J, Oberle V, Zuhorn IS, Hoekstra D (2004) Size-dependent internalization of particles via the pathways of clathrin- and caveolae-mediated endocytosis. Biochem J 377:159-69 Literatur 110 [172] Thors L, Eriksson J, Fowler CJ (2007) Inhibition of the cellular uptake of anandamide by genistein and its analogue daidzein in cells with different levels of fatty acid amide hydrolase-driven uptake. Br J Pharmacol 152:744-50 [173] Nilsson BO, Larsson A (1992) Inert carriers for immunization. Res Immunol 143:553-7; discussion 80-1 [174] Nilsson BO, Svalander PC, Larsson A (1987) Immunization of mice and rabbits by intrasplenic deposition of nanogram quantities of protein attached to Sepharose beads or nitrocellulose paper strips. J Immunol Methods 99:67-75 [175] Kalkanidis M, Pietersz GA, Xiang SD, Mottram PL, Crimeen-Irwin B, Ardipradja K, Plebanski M (2006) Methods for nano-particle based vaccine formulation and evaluation of their immunogenicity. Methods 40:20-9 [176] Frohlich E, Samberger C, Kueznik T, Absenger M, Roblegg E, Zimmer A, Pieber TR (2009) Cytotoxicity of nanoparticles independent from oxidative stress. J Toxicol Sci 34:363-75 [177] Manolova V, Flace A, Bauer M, Schwarz K, Saudan P, Bachmann MF (2008) Nanoparticles target distinct dendritic cell populations according to their size. Eur J Immunol 38:1404-13 [178] Wang X, Uto T, Sato K, Ide K, Akagi T, Okamoto M, Kaneko T, Akashi M, Baba M (2005) Potent activation of antigen-specific T cells by antigen-loaded nanospheres. Immunol Lett 98:123-30 [179] Großmann C (2008) Optimierung genetischer, auf Rezeptorvermittelter Antigenaufnahme beruhender Impfstrategien, Bochum: Ruhr-Universität [180] Schnell MA, Zhang Y, Tazelaar J, Gao GP, Yu QC, Qian R, Chen SJ, Varnavski AN, LeClair C, Raper SE, Wilson JM (2001) Activation of innate immunity in nonhuman primates following intraportal administration of adenoviral vectors. Mol Ther 3:708-22 [181] Rea D, Schagen FH, Hoeben RC, Mehtali M, Havenga MJ, Toes RE, Melief CJ, Offringa R (1999) Adenoviruses activate human dendritic cells without polarization toward a T-helper type 1-inducing subset. J Virol 73:10245-53 [182] Dietz AB, Vuk-Pavlovic S (1998) High efficiency adenovirus-mediated gene transfer to human dendritic cells. Blood 91:392-8 [183] Kameyoshi Y, Dorschner A, Mallet AI, Christophers E, Schroder JM (1992) Cytokine RANTES released by thrombin-stimulated platelets is a potent attractant for human eosinophils. J Exp Med 176:587-92 Literatur 111 [184] Arthur JF, Butterfield LH, Roth MD, Bui LA, Kiertscher SM, Lau R, Dubinett S, Glaspy J, McBride WH, Economou JS (1997) A comparison of gene transfer methods in human dendritic cells. Cancer Gene Ther 4:17-25 [185] Morelli AE, Larregina AT, Ganster RW, Zahorchak AF, Plowey JM, Takayama T, Logar AJ, Robbins PD, Falo LD, Thomson AW (2000) Recombinant adenovirus induces maturation of dendritic cells via an NF-kappaB-dependent pathway. J Virol 74:9617-28 [186] Bruder JT, Kovesdi I (1997) Adenovirus infection stimulates the Raf/MAPK signaling pathway and induces interleukin-8 expression. J Virol 71:398-404 [187] Di Paolo NC, Miao EA, Iwakura Y, Murali-Krishna K, Aderem A, Flavell RA, Papayannopoulou T, Shayakhmetov DM (2009) Virus binding to a plasma membrane receptor triggers interleukin-1 alpha-mediated proinflammatory macrophage response in vivo. Immunity 31:110-21 [188] Higginbotham JN, Seth P, Blaese RM, Ramsey WJ (2002) The release of inflammatory cytokines from human peripheral blood mononuclear cells in vitro following exposure to adenovirus variants and capsid. Hum Gene Ther 13:129-41 [189] Johannes L, Lamaze C (2002) Clathrin-dependent or not: is it still the question? Traffic 3:443-51 [190] Watts C (1997) Capture and processing of exogenous antigens for presentation on MHC molecules. Annu Rev Immunol 15:821-50 [191] Hillaireau H, Couvreur P (2009) Nanocarriers' entry into the cell: relevance to drug delivery. Cell Mol Life Sci 66:2873-96 [192] Meier O, Greber UF (2004) Adenovirus endocytosis. J Gene Med:152-63 [193] Murata M, Peranen J, Schreiner R, Wieland F, Kurzchalia TV, Simons K (1995) VIP21/caveolin is a cholesterol-binding protein. Proc Natl Acad Sci U S A 92:10339-43 [194] Scheiffele P, Verkade P, Fra AM, Virta H, Simons K, Ikonen E (1998) Caveolin-1 and -2 in the exocytic pathway of MDCK cells. J Cell Biol 140:795806 [195] Kurzchalia TV, Dupree P, Parton RG, Kellner R, Virta H, Lehnert M, Simons K (1992) VIP21, a 21-kD membrane protein is an integral component of transGolgi-network-derived transport vesicles. J Cell Biol 118:1003-14 Literatur 112 [196] Nakaoka R, Inoue Y, Tabata Y, Ikada Y (1996) Size effect on the antibody production induced by biodegradable microspheres containing antigen. Vaccine 14:1251-6 [197] Bayer W, Schimmer S, Hoffmann D, Dittmer U, Wildner O (2008) Evaluation of the Friend Virus model for the development of improved adenovirus-vectored anti-retroviral vaccination strategies. Vaccine 26:716-26 [198] Radosevic K, Rodriguez A, Lemckert A, Goudsmit J (2009) Heterologous prime-boost vaccinations for poverty-related diseases: advantages and future prospects. Expert Rev Vaccines 8:577-92 [199] Cowdery JS, Tolaymat N, Weber SP (1991) The effect of partial in vivo depletion of CD4 T cells by monoclonal antibody. Evidence that incomplete depletion increases IgG production and augments in vitro thymic-dependent antibody responses. Transplantation 51:1072-5 [200] Ye X, Robinson MB, Pabin C, Batshaw ML, Wilson JM (2000) Transient depletion of CD4 lymphocyte improves efficacy of repeated administration of recombinant adenovirus in the ornithine transcarbamylase deficient sparse fur mouse. Gene Ther 7:1761-7 [201] Furuichi Y, Tokuyama H, Ueha S, Kurachi M, Moriyasu F, Kakimi K (2005) Depletion of CD25+CD4+T cells (Tregs) enhances the HBV-specific CD8+ T cell response primed by DNA immunization. World J Gastroenterol 11:3772-7 [202] Brown SL, Miller RA, Horning SJ, Czerwinski D, Hart SM, McElderry R, Basham T, Warnke RA, Merigan TC, Levy R (1989) Treatment of B-cell lymphomas with anti-idiotype antibodies alone and in combination with alpha interferon. Blood 73:651-61 [203] Mosmann TR, Coffman RL (1989) TH1 and TH2 cells: different patterns of lymphokine secretion lead to different functional properties. Annu Rev Immunol 7:145-73 [204] Tay SS, Plain KM, Bishop GA (2009) Role of IL-4 and Th2 responses in allograft rejection and tolerance. Curr Opin Organ Transplant 14:16-22 Dissertationsbezogene bibliographische Daten 8 113 Dissertationsbezogene bibliographische Daten Publikationen Bayer W.,Tenbusch M., Lietz R., Johrden L., Schimmer S., Überla K. U., Dittmer U., Wildner O. (2010) Vaccination with an adenoviral vector that encodes and displays a retroviral antigen induces improved neutralizing antibody and CD4+ Tcell responses and confers enhanced protection Journal of Virology 84: 1967-1976 Poster Johrden L., Bayer W., Tenbusch M., Lietz R., Wildner O. (2010) Evaluation of antigen-coated nanoparticles for vaccination purposes (Poster 649) 4th European Congress of Virology, Italien 113 Lebenslauf 9 114 Lebenslauf Persönliche Daten Adresse: Rellinghauserstr. 279 45136 Essen Geburtsdatum 13.07.1983 Staatsangehörigkeit Deutsch Familienstand ledig Schule und Studium 08/92-06/02 Maria-Wächtler Gymnasium Essen 10/02-10/07 Studium 10/02-08/05 Bachelor of Science Biologie Arbeitsgruppe Verhaltensbiologie Ruhr-Universität Bochum Titel: „Einfluss der Pollenzufuhr auf das Sammelverhalten der Honigbiene Apis mellifera“ 10/05-10/07 Master of Science Biologie Arbeitsgruppe Zoologie/Parasitologie Ruhr-Universität Bochum Titel: „Antimikrobielle Faktoren der Feuerwanze Pyrrhocoris apterus (Hemiptera: Pyrrhocoridae): Effekt des Flagellaten Leptomonas pyrrhocoris (Kinetoplastida: Trypanosomatidae)“ 12/07- bis jetzt Promotion (Dr. rer. nat.) Abteilung für Molekulare und Medizinische Virologie Ruhr-Universität Bochum voraussichtliches Datum der Verteidigung: April 2011 Titel: „Vergleichende Studien von Antigen-beladenen Nanopartikeln und UV-inaktivierten Adenoviren in einem Protein-basierenden Immunisierungs-Ansatz im Ovalbumin-Modell“ Lebenslauf 1 Erklärung Hiermit erkläre ich, dass ich die Arbeit selbständig verfasst, bei keiner anderen Fakultät eingereicht und dass ich keine anderen als die angegebenen Hilfsmittel verwendet habe. Es handelt sich bei der heute von mir eingereichten Dissertation um fünf in Wort und Bild völlig übereinstimmende Exemplare. Weiterhin erkläre ich, dass digitale Abbildungen nur die orignalen Daten enthalten und in keinem Fall inhaltsverändernde Bildbearbeitung vorgenommen wurde. Essen, den 28.01.2011