Die Rolle des NS1-Proteins hoch pathogener aviärer
Werbung

ABTEILUNG VIROLOGIE
INSTITUT FÜR MEDIZINISCHE MIKROBIOLOGIE UND HYGIENE
DER ALBERT-LUDWIGS-UNIVERSITÄT
FREIBURG IM BREISGAU
Die Rolle des NS1-Proteins hoch pathogener aviärer
Influenza-A-Viren im Huhn
INAUGURAL-DISSERTATION
zur
Erlangung der Doktorwürde
der Fakultät für Biologie
der Albert-Ludwigs-Universität
Freiburg im Breisgau
vorgelegt von
Nicola Penski
geboren in München
Januar 2010
Dekan:
Prof. Dr. A. Aertsen
Promotionsvorsitzender:
Prof. Dr. E. Schäfer
Referent:
Prof. Dr. P. Stäheli
Koreferent:
Prof. Dr. M. Schwemmle
Tag der Verkündung des Prüfungsergebnisses: 27.04.2010
Danke…
… an Prof. Dr. Peter Stäheli, dass ich diese Arbeit in seinem Labor anfertigen durfte.
Durch seine intensive, motivierende Betreuung hat er maßgeblich zum Gelingen dieser
Arbeit beigetragen.
… an Prof. Dr. Georg Kochs für seine hilfreiche Einarbeitung und vor allem für alle
praktischen Tipps, die das Experimentieren sehr vielseitig gemacht haben.
… an alle Kooperationspartner in München (Carsten Krohmann, Sonja Kothlow und
Bernd Kaspers), auf Riems (Thomas Vahlenkamp, Anne Carnitz, Angele Breithaupt,
Katharina Brehm und Jürgen Stech) und in Mittelhäusern (Nicolas Ruggli und Artur
Summerfied), ohne die ein großer Teil dieser Arbeit nicht möglich gewesen wäre.
… an das Trio aus Vancouver für die schöne Zeit während des Kongresses und vor
allem danach.
… vor allem an Iris Körner, Petra Zimmermann, Daniela Kugel und unseren
hochwohlgeborenen Alex Freiherr von der Malsburg für die schöne Zeit im und
außerhalb des Labors und die vielen „sinnigen“ und „unsinnigen“ Gespräche.
… an alle Stähelis, Kochs, Friedemänner, Schwemmles und an alle Ehemaligen, die
uns in der Zwischenzeit verlassen haben für die super Arbeitsatmosphäre, die ständige
Hilfsbereitschaft und die unterhaltsamen Kaffeepausen, die den Laboralltag wesentlich
bereicherten.
… an Matthias, der mich vor allem außerhalb des Labors unterstützt hat, stets ein
offenes Ohr für meine großen und kleinen Probleme hatte und immer an mich
geglaubt hat. Ohne ihn hätte ich diese Zeit nur halb so gut überstanden.
… auch an meine Eltern Ellen und Siegfried, die mich die ganzen Jahre über
unterstützt haben und jederzeit für mich da waren.
Beiträge zu wissenschaftlichen Tagungen
I.
Dritter europäischer Kongress für Virologie
Nürnberg (Deutschland), 1.-5. September 2007
Penski N, Kothlow S, Ruggli N, Summerfield A, Martinez L, Garcia-Sastre A,
Kaspers B, Stech J, Kochs g, and Staeheli P.
Role of the NS1 protein of avian influenza A virus strain SC35 (H7N7) in cell
culture and in chickens
Art der Präsentation: Poster
II.
Jahrestagung der Gesellschaft für Virologie
Heidelberg (Deutschland), 5.-8. März 2008
Penski N, Kothlow S, Ruggli N, Zimmermann P, Summerfield A, Kaspers B, Stech J,
Kochs G, and Staeheli P.
The NS1 protein of influenza A virus strain SC35 confers virulence in adult
chickens
Art der Präsentation: Poster
III.
The American Society for Virology, 28th annual meeting
Vancouver (Kanada), 11.-15. Juli 2009
Penski N, Krohmann C, Kothlow S, Gohrbandt S, Hundt J, Veits J, Breithaupt A,
Stech J, Kochs G, Ruggli N, Summerfield A, Vahlenkamp T, Kaspers B, Staeheli P.
NS1 proteins of pathogenic avian influenza viruses do not suppress interferon
synthesis in chickens but rather block interferon action
Art der Präsenation: Vortrag
IV.
5th Orthomyxovirus Research Conference
Freiburg (Deutschland), 9.-12. September 2009
Penski N, Krohmann C, Kothlow S, Gohrbandt S, Hundt J, Veits J, Breithaupt A,
Stech J, Kochs G, Ruggli N, Summerfield A, Vahlenkamp T, Kaspers B, Staeheli P.
NS1 proteins of pathogenic avian influenza viruses do not suppress interferon
synthesis in chickens but rather block interferon action
Art der Präsentation: Vortrag
Abkürzungen
A
…… Amp
Amp
B
C
D
E
Ampicillin
r
Ampicillin-Resistenz
AP-1
activator protein 1
APS
Ammoniumpersulfat
AS
Aminosäure
…… bidest
bidestilliert
bp
Basenpaar
BSA
bovines Serumalbumin
…… CARD
caspase-recruiting domain
CARDIF
CARD adaptor inducing IFN-β
cDC
conventional dendritic cell
cDNA
complementary DNA
CEF
chicken embryo fibroblast
CPE
cytopathic effectt
CPSF
cleavage and polyadenylation specificity factor
…… d
day
DC
dendritic cell
DMEM
Dulbecco’s modified Eagle Medium
DMSO
Dimethylsulfoxid
DNA
desoxyribonucleicacid
ds
double stranded
dsRNA
Doppelstrang-RNA
dCTP
Desoxycytidintriphosphat
…… E. coli
Escherichia coli
EDTA
Ethylendiamintetraacetat
eIF-2α
eukaryotischer Translationsinitiationsfaktor 2α
eIF4GI
eukaryotischer Translationsinitiationsfaktor 4GI
F
…… FF-Luc
firefly-Luziferase
ffu
focus forming unit
FKS
fötales Kälberserum
for
forward
G
…… g
Gravitationskraft
H
…… h
hour
I
HA
Hämagglutinin
HEPES
N-2-Hydroxyethylpiperazin-N’-2-Ethansulfonsäure
HPAIV
highly pathogenic avian influenza virus
HRP
horse radish peroxidase
…… IBV
infectious bronchitis virus
IFN
Interferon
IκB
inhibitor of NF-κB
IKK
IκB-related kinase
IL
Interleukin
IPS-1
interferon-β promoter stimulator 1
IPTG
Isopropylthio-β-galaktosid
IRAK
IL1-R associated kinase
IRF
interferon regulatory factor
ISGF3
IFN-stimulated gene factor 5
ISG
interferon stimulated gene
ISRE
interferon stimulated response element
J
…… JAK
Janus-Kinase
K
…… kb
kilo Basenpaare
kDa
L
kilo Dalton
…… LB-Medium Luria-Bertani-Medium
LD50
lethal dose 50
LPAIV
low pathogenic avian influenza virus
M
N
O
P
LPS
Lipopolysaccharid
Luc
Luziferase
…… M
......
Matrixprotein
MAVS
mitochondrial antiviral signaling
MDA-5
melanoma differentiation-associated gene 5
MDV
Mareks disease virus
MHC
major histocompatibility complex
mock
nicht infiziert (engl. vortäuschen)
MOI
multiplicity of infection
MOPS
3-Morpholinopropansulfonsäure
mRNA
messenger RNA
Mx
myxovirus resistance
MyD88
myeloid differentiation primary response gene 88
NA
Neuraminidase
NaCl
Natriumchlorid
NCR
non coding region
NDV
Newcastle disease virus
NEP
nuclear export protein
NF-κB
nuclear factor κB
NK-Zellen
natürliche Killerzellen
NLS
nuclear localisation signal
NO
Nitritoxid
NP
Nukleoprotein
NS
Nichtstrukturprotein
Nt
Nukleotid
…… OAS
2’,5’-Oligoadenylat-Synthetase
OD
optische Dichte
ORF
open reading frame
…… PA
p.a.
polymerase acidic protein
pro analysi
Q
PABP
poly A binding protein
PAMP
pathogen associated molecular pattern
PB1
polymerase basic protein 1
PB2
polymerase basic protein 2
PBS
phophate buffered saline
PCR
polymerase chain reaction
pDC
plasmacytoid dendritic cell
PIPES
Piperazin-N,N’2bis(ethansulfonsäure)
PKR
IFN-inducible dsRNA-dependent protein kinase R
PRR
pattern recognition receptor
…… qPCR
qRT-PCR
R
S
T
…… Ren
quantitative PCR
quantitative real-time PCR
Renilla
Ren-Luc
Renilla-Luziferase
rev
reverse
RIG-I
retinoid acid inducible gene 1
RNA
ribonucleicacid
RNP
Ribonukleoprotein
rpm
revolutions per minute
RT
reverse Transkriptase/ Transkription
RT-PCR
real-time PCR
…… SDS
Natriumdodecylsulfat
ss
single stranded
ssRNA
single stranded RNA
STAT
signal transducer and activator of transcription
SV40
Simian Virus 40
…… TAE
Tris-Acetat-EDTA
Taq
Thermus aquaticus
TBK-1
TANK binding kinase-1
TEMED
N,N,N,N-Tetramethylethylendiamin
TLR
toll-like receptor
TNF-α
Tumornekrosefaktor-α
TOC
tracheal ogan culture
TRIF
Toll-IL-1 receptor-domain-containing adaptor-inducing
interferon β
U
V
W
Tris
Tris-(hydroximethyl)aminomethan
Tyk
Tyrosinkinase
…… U
Unit
UTR
untranslated region
UV
ultraviolett
…… VISA
virus-induced signaling adaptor
vRNA
virale RNA
vRNP
virales Ribonukleoprotein
VSV
vesicular stomatitis virus
…… wt
Wildtyp
Inhaltsverzeichnis
Inhaltsverzeichnis
1. Zusammenfassung
1
2. Einleitung
3
2.1 Das angeborene Immunsystem
3
2.1.1 Die Typ I Interferone
4
2.1.2 Virale Infektionen induzieren die Sekretion von Typ I Interferonen
4
2.1.3 Die Weiterleitung des Interferon-Signals
7
2.1.4 Interferon-stimulierte Genprodukte mit antiviraler Aktivität
8
2.1.5 Das aviäre angeborene Immunsystem
9
2.1.5.1 Die Zellen des aviären angeborenen Immunsystems
9
2.1.5.2 Die Interferone des Huhns
10
2.1.5.3 Die Toll-like Rezeptoren im Huhn
11
2.1.5.4 Interferon-induzierte Gene im Huhn
12
2.2 Das Influenza-A-Virus
13
2.2.1 Partikel- und Genomstruktur der Influenza-A-Viren
14
2.2.5 Das NS1-Protein der Influenza-A-Viren
16
2.2.3 Aviäre Influenza-A-Viren
20
2.2.4 Die Übertragung von Influenza-A-Viren
21
2.3 Das Krankheitsbild beim Huhn
21
2.4 Zielsetzung der Arbeit
22
3. Material und Methoden
24
3.1 Chemikalien
24
3.2 Proteinmethoden
25
3.3 Zellkulturmaterial
25
3.4 Transfektionsreagenzien
26
3.5 Sonstige Materialien
26
3.6 Geräte
26
E
Inhaltsverzeichnis
3.7 Enzyme und Größenstandards
27
3.8 Kit-Systeme
28
3.9 Radioaktivität
28
3.10 Puffer und Nährmedien
28
3.10.1 Behandlung von Lösungen und Geräten
28
3.10.2 Puffer
28
3.10.3 Nährmedien für Bakterien
33
3.10.4 Zellkulturmedien
34
3.10.6 Anästhesie der Versuchstiere
35
3.11 Bakterien
35
3.12 Viren
35
3.13 Interferone
36
3.14 Zellen
36
3.15 Mausstämme
36
3.16 Antikörper
36
3.17 Oligonukleotide
37
3.18 Plasmide
39
3.19 Zellkulturarbeiten und virologische Methoden
40
3.19.1 Zellkultivierung
40
3.19.2 Herstellung von Trachealorgankulturen aus Hühnerembryonen
40
3.19.3 Transfektion
40
3.19.4 Dualer Luziferase-Reportertest
41
3.19.5 Infektion mit Influenza-A-Viren für Wachstumskurven
41
3.19.6 Herstellung rekombinanter Influenza-A-Viren
42
3.19.7 Immunfärbung für die Virustiterbestimmung
43
3.19.8 Virusinaktivierung
43
3.19.9 Bioassay zur Detektierung von induziertem Hühner-Interferon
44
3.20 DNA-Standardtechniken
3.20.1 Minipräparation von Plasmid-DNA
44
44
E
Inhaltsverzeichnis
3.20.2 Midipräparation von Plasmid-DNA
45
3.20.3 Restriktionsverdau
45
3.20.4 Agarose-Gelelektrophorese
45
3.20.5 Gelextraktion
45
3.20.6 PCR (polymerase chain reaction)
46
3.20.7 TOPO® TA Cloning von PCR-Produkten
46
3.20.8 Dephosphorylierung linearisierter Plasmid-DNA
47
3.20.9 Ligation von DNA-Fragmenten
47
3.20.10 DNA-Sequenzierung
48
3.20.11 Ortsspezifische Mutagenese
48
3.20.12 Quantitative PCR (qPCR)
49
3.21 RNA-Methoden
51
3.21.1 RNA-Extraktion
51
3.21.2 cDNA-Synthese
51
3.21.3 Northern Blot
52
3.21.3.1 Präparation der RNA-Proben und Gelelektrophorese
52
3.21.3.2 Transfer der RNA
52
3.21.3.3 Herstellung einer radioaktiven DNA-Sonde
53
3.21.3.4 Hybridisierung
53
3.22 Mikrobiologische Methoden
53
3.22.1 Herstellung kompetenter Bakterien
53
3.22.2 Transformation von Bakterien
54
3.22.3 Kultivierung von Bakterien
54
3.23 Proteinbiochemische Methoden
54
3.23.1 Herstellung von Zelllysaten für Western Blot
54
3.23.2 Proteinelektrophorese im SDS-Polyacrylamidgel
55
3.23.3. Western-Blot
55
3.23.4. IFN-β-ELISA
55
3.23.5. Influenza-A-Virus-Nukleoprotein-basierter ELISA
56
3.23.6. Immunhistochemische Färbung
56
E
Inhaltsverzeichnis
3.23.7 Hühner-Interferon-Aufreinigung aus E.coli
3.24 Tierexperimentelle Methoden
56
57
3.24.1. Mausexperimente
57
3.24.1.1 Infektion der Versuchstiere
57
3.24.1.2 Herstellung von Organhomogenaten
58
3.24.2 Hühnerexperimente
58
3.24.2.1 Infektion der Versuchstiere
58
3.24.2.2 Herstellung von Organhomogenaten
59
4. Ergebnisse
60
4.1 Wachstumsverhalten und Interferon-Induktion von SC35-wt (H7N7) und Mutanten in
Zellkultur und verschiedenen in vivo-Systemen
60
4.1.1 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten SC35-Viren in Hühnerzellen
61
4.1.2 Herstellung von Trachealorgankulturen als ex vivo-System
65
4.1.3 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten SC35-Viren in Trachealorgankulturen
66
4.1.4 Untersuchung der Interferon-Induktion von SC35-wt und SC35-delNS1 in
Luziferase-Reporter-Mäusen
68
4.1.5 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion von SC35wt und SC35-delNS1 in adulten Hühnern
69
4.1.6 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten SC35-Viren in adulten Hühnern zu früheren Zeitpunkten
73
4.1.7 Interferon-Sensitivität der rekombinanten SC35-Viren in Hühnerzellen
74
4.1.9 Interferon-Sensitivität von SC35 und SC35-NS1(126) in Trachealorgankulturen 76
4.2 Wachstumsverhalten und Interferon-Induktion von R65-wt (H5N1) und Mutanten in
Zellkultur und verschiedenen in vivo-Systemen
77
4.2.1 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten R65-Viren in Hühnerzellen
78
4.2.2 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten R65-Viren in Trachealorgankulturen
81
4.2.3 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten R65-Viren in Mx-positiven Mäusen
82
4.2.4 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten R65-Viren in adulten Hühnern
84
E
Inhaltsverzeichnis
4.2.5 Interferon-Sensitivität der rekombinanten R65-Viren in Hühnerzellen
88
4.2.6 Interferon-Sensitivität von R65-wt und R65-trunkNS1 in Trachealorgankulturen 88
4.2.6 Interferon-Sensitivität der rekombinanten R65-Viren in Säugerzellen
89
4.2.8 Interferon-Sensitivität von R65-wt in Mx-positiven Mäusen
90
4.2.9 Interferon-Sensitivität von R65-wt in adulten Hühnern
91
4.2.10 Einfluss des NS1-Proteins von R65 auf den Interferon-Signalweg
92
5. Diskussion
95
5.1 Generierung der verwendeten Viren
95
5.2 Wachstumsverhalten
96
5.3 Interferon-Induktion
97
5.4 Interferon-Sensitivität
101
5.5 Einfluss des NS1-Proteins von R65 auf den Interferon-Signalweg
104
5.6 Ausblick
105
6. Literatur
106
E
1
Zusammenfassung
1. Zusammenfassung
Das natürliche Reservoir von Influenza-A-Viren bilden Wasservögel. Die hohe genetische
Variabilität erlaubt es den Viren jedoch, die Speziesbarrieren zu überwinden, sich an neue
Wirte anzupassen und in diesen schwere Erkrankungen auszulösen. Für die Inhibierung der
Virusreplikation und den Verlauf einer Erkrankung sind das angeborene Immunsystem und
die
durch
Interferon
(IFN)
induzierten
Gene
von
größter
Bedeutung.
Das
Nichtstrukturprotein 1 (NS1) der Influenza-A-Viren ist ein wichtiger Virulenzfaktor. Es
interagiert mit dem angeborenen Immunsystem des Wirtes, indem es unter anderem die
virusinduzierte IFN-Antwort inhibiert. Im Hühnersystem war bisher jedoch noch sehr wenig
über die frühe Immunantwort und wichtige Wirtsfaktoren bekannt, die während der
Induktionsphase der Abwehr eine Rolle spielen.
Um das Zusammenspiel zwischen dem NS1-Protein hoch pathogener Influenza-A-Viren mit
ihrem eigentlichen Wirt, dem Huhn, zu untersuchen, wurden rekombinante Varianten der
hoch pathogenen Influenza-A-Virusstämme SC35 (H7N7) und R65 (H5N1) generiert. Des
Weiteren wurden Virusmutanten hergestellt, bei denen NS1 entweder komplett deletiert
wurde (delNS1) oder C-terminal verkürzt ist. Diese Virusmutanten waren in HühnerembryoFibroblasten leicht attenuiert und induzierten eine stärkere IFN-Antwort als die Wildtyp (wt)Viren. Ähnliche Ergebnisse lieferte die Infektion von Mäusen. Ein erster Unterschied zeigte
sich bei der Infektion von kultiviertem Trachealgewebe von Hühnerembryonen. Mutanten
ohne NS1 waren überhaupt nicht in der Lage zu wachsen, während Mutanten mit C-terminal
verkürztem
NS1
relativ
gut
replizierten.
Bei
der
IFN-Induktion
zeigte
sich
überraschenderweise, dass die wt-Stämme genauso viel IFN induzierten wie die delNS1Viren. Ein noch drastischeres Bild zeigte sich, als adulte Hühner mit den diversen Viren
infiziert wurden. Die delNS1-Viren waren hoch attenuiert. Im Gegensatz dazu waren die
Mutanten mit C-terminal verkürztem NS1 virulent und im Fall der H5N1-Mutante sogar in
der Lage, Hühner zu töten, wenn auch langsamer als das wt-Virus. Erstaunlicherweise
induzierten die wt-Viren viel mehr IFN in der Lunge und in anderen Geweben als die NS1Mutanten. Um die überraschend hohe Resistenz der wt-Viren gegenüber endogenem HühnerIFN zu erklären, wurde die IFN-Sensitivität der Viren getestet. Die Vorbehandlung von
Hühnerzellen mit Hühner-IFN-α inhibierte die Replikation der wt-Viren kaum, hatte aber
einen starken Einfluss auf die Replikation der Mutanten. In adulten Hühnern schützte die
Behandlung mit hohen Dosen an Hühner-IFN-α vor und nach der Infektion hingegen nicht
E
2
Zusammenfassung
vor einer Infektion mit H5N1-wt. Im Gegensatz dazu führte eine IFN-Behandlung von
Mäusen zu einer kompletten Hemmung der Virusreplikation.
Zusammengefasst deuten die Daten darauf hin, dass die eigentliche Rolle des NS1-Proteins
im Huhn nicht die Unterdrückung der IFN-Antwort ist, und dass das Typ I IFN-System des
Huhns nicht in der Lage ist, diese Tiere vor hoch pathogenen aviären Influenza-A-Viren zu
schützen. Diese Ergebnisse zeigen somit, dass es prinzipielle Unterschiede in der Rolle des
viralen NS1-Proteins in Vögeln und Säugern gibt.
E
3
Einleitung
2. Einleitung
Das immer wiederkehrende Auftreten von Influenza-Epidemien und -Pandemien macht
deutlich, dass immer noch wenig über die Mechanismen bekannt ist, welche die Pathogenität
und Übertragung von Influenza-Viren bestimmen. Das erst seit kurzem zirkulierende, vom
Schwein abstammende Influenza-A-Virus (H1N1), das sich durch eine sehr rasche und
effektive Mensch-zu-Mensch-Übertragung auszeichnet, ist ein weiterer Beweis dafür, dass
weitere Studien über die Pathogenese und die Adaptation von Influenzaviren an andere Wirte
nötig sind (160).
Bis heute ist sehr viel über das Zusammenspiel von Influenza-A-Viren mit dem Immunsystem
der Maus oder des Menschen bekannt. Vor allem die Maus ist ein oft genutztes Modell, um
die Fähigkeit von Influenzaviren, Morbidität und Mortalität zu induzieren, zu charakterisieren
und zu quantifizieren. Auch die Kontrolle durch das Immunsystem wird oft in der Maus
untersucht, obwohl diese kein natürlicher Wirt ist. Ein weiterer Nachteil des Mausmodells ist,
dass das Virus nicht von Tier zu Tier übertragen wird. Außerdem sind viele hoch pathogene
Influenzaviren nicht in der Lage, Krankheit in Mäusen auszulösen, ohne vorher durch
mehrere Passagen an die Maus adaptiert worden zu sein (142). Deshalb ist es wichtig, die
Pathogenese aviärer Influenzaviren im eigentlichen Wirt zu untersuchen
2.1 Das angeborene Immunsystem
Die meisten Infektionen, die wir im Laufe unseres Lebens bekommen, verlaufen im
Allgemeinen harmlos und oft unbemerkt. In vielen Fällen werden die eindringenden
Mikroorganismen und Viren ohne weitere Probleme vom Körper eliminiert. Einer der
Hauptgründe dafür, dass diese Pathogene größtenteils keinen Schaden anrichten, liegt in der
angeborenen Immunantwort (71). Diese ist, im Gegensatz zur erworbenen Immunität, für die
frühe und unmittelbare Pathogenerkennung nach dem Eindringen von Mikroorganismen
verantwortlich. Das angeborene Immunsystem erkennt bestimmte molekulare Strukturen der
eindringenden Organismen, die in den eigenen Geweben nicht vorhanden sind (150). Vor
allem das Interferon (IFN)-System ist in der Lage, durch seine schnelle Aktivierung die
Ausbreitung von intrazellulären Krankheitserregern zu verhindern und die Zeitspanne zu
überbrücken, bis der Schutz durch das adaptive Immunsystem zum Tragen kommt. Da viele
Viren jedoch Strategien entwickelt haben, um die IFN-Antwort zu umgehen oder zu
unterdrücken, sind sie oft dennoch in der Lage, zu replizieren und Krankheiten auszulösen.
E
4
Einleitung
Das angeborene Immunsystem erkennt bestimmte molekulare Strukturen der eindringenden
Organismen, die als fremd detektiert werden und nicht in den eigenen Geweben vorhanden
sind (150). Diese molekularen Strukturen werden als so genannte PAMPs (pathogen
associated molecular patterns) bezeichnet und finden sich z.B. in Proteinen und
Nukleinsäuren und sind meist essentiell für das Überleben der Pathogene (244). Das
Immunsystem des Wirtsorganismus besitzt nun verschiedene PRRs (pattern recognition
receptors), die diese PAMPs erkennen (171).
2.1.1 Die Typ I Interferone
Typ I Interferone als antivirale Faktoren wurden vor ungefähr 50 Jahren von Isaacs und
Lindenmann
entdeckt.
Nach
Inkubation
von
Hühnerzellen
mit
hitzeinaktivierten
Influenzaviren entdeckten sie einen sezernierten Faktor, der die Zellen gegen weitere
Infektionen resistent machte und nannten diesen Interferon, da er mit der Replikation der
Viren interferierte (88).
Interferone sind eine große Familie von induzierbaren Zytokinen, von denen die meisten
antivirale Aktivität besitzen und ausschließlich in Vertebraten zu finden sind (88, 181). Zu
den Typ I Interferonen gehören IFN-α und IFN-β, aber auch die weniger untersuchten IFN-ω,
IFN-κ und IFN-τ (144, 193). Neben den Typ I Interferonen gibt es noch zwei weitere Klassen:
das Typ II IFN-γ (5, 85, 180) und die Typ III Interferone, welche die erst kürzlich
identifizierten IFN-λ 1-3 umfassen (119, 208, 246). Die Typ II Interferone werden eher von
aktivierten T-Zellen und NK (natürliche Killer)-Zellen produziert, Typ I und III Interferone
hauptsächlich von infizierten Zellen.
Man geht davon aus, dass Typ I Interferone die erste Barriere der Wirtsabwehr darstellen
(245). Sie wirken aber auch als Immunmodulatoren des adaptiven Immunsystems, indem sie
z.B. NK-Zellen, Makrophagen oder dendritische Zellen (DCs) aktivieren (14, 181).
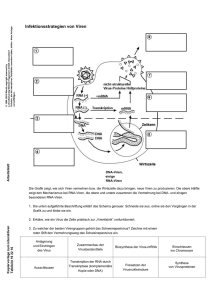
2.1.2 Virale Infektionen induzieren die Sekretion von Typ I Interferonen
Die Induktion von IFN-α/β, die die Hauptgruppe der Typ I Interferone darstellen, ist sehr
stark reguliert. Es gibt zwei Hauptwege, durch die die Produktion induziert wird. Die meisten
Zellen des Körpers, wie z.B. Fibroblasten, Hepatozyten und cDCs (conventional dendritic
cells) verwenden den klassischen Signalweg, während in pDCs (plasmacytoid dendritic cells)
nach einer Virusinfektion der so genannte TLR (toll-like receptor)-Signalweg initiiert wird.
E
5
Einleitung
Der klassische Signalweg (Abbildung 2.1):
Beim so genannten klassischen Signalweg wird die Signalkaskade durch virale
doppelsträngige
RNA
(dsRNA)
beziehungsweise
5’triphosphorylierte
RNA
mit
Doppelstrangcharakter induziert. Zwei intrazelluläre Helikasen, RIG-I (retinoid acid
inducible gene 1) (264) und MDA-5 (melanoma differentiation-associated gene 5) (3) dienen
als Sensoren für diese RNAs. Die Bindung der RNA führt dazu, dass ein Adapterprotein,
welches IPS-1 (interferon-β promoter stimulator 1) (100), MAVS (mitochondrial antiviral
signaling) (207), VISA (virus-induced signaling adaptor) (262) oder CARDIF (CARD
adaptor inducing IFN-β) (153) genannt wird, mit den Helikasen interagiert. Die Aktivierung
weiterer Kinasen führt zur Phosphorylierung des Transkriptionsfaktors IRF-3 (interferon
regulatory factor 3) (48). Dieser wandert als Dimer in den Zellkern und initiiert zusammen
mit verschiedenen Transkriptionskoaktivatoren die IFN-β-mRNA (messenger RNA)-Synthese
(79). Nach dieser ersten Welle kommt es zur Expression des Transkriptionsfaktors IRF-7, der
in den meisten Zellen, abgesehen von pDCs, nur in sehr geringen Mengen vorkommt (197).
Es wurde gezeigt, dass IRF-7 auf dem gleichen Weg wie IRF-3 aktiviert wird und als
Hauptregulator der IFN-Genexpression dafür verantwortlich ist, dass in einer zweiten Welle
IFN-β, IFN-α4 und andere IFN-α-Subtypen transkribiert werden (196).
Einige Zellen des hämatopoetischen Systems, wie z.B. cDCs exprimieren TLR3 (Toll-like
receptor 3) und erkennen virale und andere dsRNA in endosomalen Kompartimenten. Die
Bindung von dsRNA an TLR3 führt über Adapterproteine zur Phosphorylierung von IRF-3
und zur darauf folgenden Sekretion von IFN-β.
Als letztes gibt es noch die PKR (IFN-inducible dsRNA-dependent protein kinase R), die in
der
Lage
ist,
dsRNA
zu
erkennen
und
ebenfalls
über
Adaptermoleküle
den
Transkriptionsfaktor NF-κB (nuclear factor κB) zu aktivieren. Dieser Weg trägt zur
Aktivierung des IFN-β-Promotors bei (123).
E
6
Einleitung
IFN-β
Virus
5‘-pppRNA
dsRNA
dsRNA
PKR
MDA-5
RIG-I
TLR3
TRAF
IPS-1
IKK α/β
TBK-1 / IKKε
TRIF
IFN-β
NF-κB
IRF-3
-3
IFN-β
Abbildung 2.1: Schematische Darstellung der IFN-β-Induktion
Doppelsträngige RNA (dsRNA) beziehungsweise 5’triphosphorylierte RNA mit Doppelstrangcharakter (5’-pppRNA) führt
zu Aktivierung der Transkriptionsfaktoren NF-κB, IRF-3 und AP-1 (nicht gezeigt). Das Zusammenspiel dieser Faktoren ist
für die Aktivierung des IFN-β-Promotors nötig. IRF-3 wird durch die Kinasen IKKε und TBK-1 phosphoryliert, welche
durch RIG-I, MDA-5 und IPS-1 aktiviert werden. Ein zweiter Signalweg besteht aus endosomalen TRL3 und TRIF
[verändert nach (71)].
Der TLR-Signalweg (Abbildung 2.2):
Ein großer Teil des im Organismus nach einer Infektion produzierten IFN-α wird von
spezialisierten Zellen, den pDCs, sezerniert (28). pDCs wurden schon früh entdeckt und
aufgrund ihrer Morphologie als plasmazytoide Zellen beschrieben. Später wurde gezeigt, dass
diese Zellen in der Lage sind, nach Virusinfektion große Mengen an Typ I Interferonen zu
produzieren. Die Besonderheit von pDCs liegt darin, dass sie verschiedene TLRs (TLR7, 8, 9)
(91) und IRF-7 konstitutiv exprimieren, wodurch eine sehr schnelle Reaktion auf
eindringende fremde Strukturen ermöglicht wird (13, 16). Die Aktivierung von TLR7 oder 8,
die ssRNA (single stranded RNA) erkennen, beziehungsweise TLR9, der unmethylierte CpGDNA erkennt, führt zu Interaktion mit dem Adapterprotein MyD88 (myeloid differentiation
primary response gene 88), was zur Bildung eines Multiproteinkomplexes führt. Nach der
Phosphorylierung von IRF-7 wandert dieser Transkriptionsfaktor als Dimer in den Zellkern
und aktiviert dort vor allem die IFN-α-Gene (91, 243).
E
7
Einleitung
TLR7/8 (ssRNA)
TRL9 (CpG DNA)
MyD88
IRAK-4
TRAF6
IRF-7
IRAK-1
IRF-7
-7
IFN-α
Abbildung 2.2: Schematische Darstellung des TLR-Signalwegs für die IFN-α-Produktion in pDCs
TLR7 und TLR8 reagieren auf RNA-Viren mit der Erkennung von ssRNA in Endosomen. TLR9 erkennt CpG-reiche
Sequenzen im Genom von DNA-Viren. Die Rezeptoren leiten das Signal über einen Multiproteinkomplex weiter, der unter
anderem das Adapterprotein MyD88 und den Transkriptionsfaktor IRF-7 enthält [verändert nach (71)].
2.1.3 Die Weiterleitung des Interferon-Signals
Sezerniertes IFN-α und IFN-β binden an den Typ I IFN-Rezeptor (IFNAR), der sich auf den
meisten Zelltypen befindet. Die IFN-induzierte Heterodimerisierung des Rezeptors (IFNAR
1/2) führt zu einer Konformationsänderung, die dafür sorgt, dass die Tyrosinkinase 2 (Tyk2)
und STAT2 (signal transducer and activator of transcription 2) an IFNAR1 binden können.
Durch die anschließende Phosphorylierung von STAT1 kommt es zur Bildung eines
STAT1/2-Heterodimers (184, 220, 233), das nach Bindung an IRF-9 (233) in den Zellkern
wandert. Dieser trimere Komplex, der ISGF3 (IFN-stimulated gene factor 3) genannt wird,
bindet an das ISRE (IFN-stimulated response element), das Bestandteil von Promotoren vieler
IFN-abhängiger Gene ist und induziert auf diese Weise die Transkription von so genannten
ISGs (IFN-stimulated genes), von denen viele antivirale Wirkung haben. (Abbildung 2.3 zeigt
einen Überblick über die beschriebene Signalkaskade.)
E
8
Einleitung
Virus
IFN-β
Virus
IFNAR
IFN-α/β
5‘-pppRNA
dsRNA
dsRNA
PKR
MDA-5
JAK-1 / TYK-2
dsRNA
RIG-I
TLR3
OAS
Mx
PKR
TRAF
IPS-1
STAT-1 -2
TRIF
IRF-7
-3
IFN-β
IKK α/β
IRF-9
TBK-1 / IKKε
ISGF-3
NF-κB
IRF-3
IFN-β
-3
IFN-α
ISRE
ISG
IFN-β
Abbildung 2.3: Schematische Darstellung des IFN-Signalwegs
Linker Teil: siehe Abbildung 2.1 Rechter Teil: Neu synthetisiertes IFN-β bindet an den Typ I IFN-Rezeptor und aktiviert die
Expression verschiedener ISGs über den JAK/STAT-Signalweg. IRF-7 amplifiziert die IFN-Antwort. Mx, OAS und PKR
sind Beispiele von Proteinen, deren Expression durch IFN induziert wird und die antivirale Aktivität besitzen [verändert nach
(71)].
2.1.4 Interferon-stimulierte Genprodukte mit antiviraler Aktivität
Typ I Interferone aktivieren die Expression von mehreren hundert ISGs (36, 38). Zu den
bekanntesten und am besten untersuchten ISG-Produkten mit antiviraler Aktivität gehören das
Mx (myxovirus resistance)-Protein, PKR und die 2’-5’-Oligoadenylat-Synthetase (OAS).
Mx-Proteine gehören zu der Superfamilie der Dynamin-ähnlichen, großen GTPasen. Sie
wurden durch die Beobachtung identifiziert, dass bestimmte Mausstämme resistent gegenüber
Vertretern der Orthomyxoviren sind. Es wurde gezeigt, dass dieser Resistenz ein intaktes
Mx1-Gen zu Grunde liegt (69, 135, 136). Genetische Analysen zeigten, dass dieses Gen nur
in Wildmäusen und in dem Inzuchtstamm A2G vollständig und funktionell ist, wohingegen
die meisten anderen Inzuchtstämme ein defektes Mx-Gen tragen (216). Das murine Mx1Protein ist im Nukleus lokalisiert, während sich Mx2 (219) und die humanen Mx-Varianten
MxA und MxB hauptsächlich im Zytoplasma befinden. Es wurde vor allem für Vertreter der
Orthomyxoviren gezeigt, dass sie sensitiv gegenüber der Wirkung von Mx1-Proteinen sind
(70, 72, 217). Humanes MxA-Protein inhibiert Mitglieder der Orthomyxoviren (173),
Paramyxoviren (200), Rhabdoviren (173), Bunyaviren (52) und Togaviren (128). Für die
Abwehr von Influenza-A-Viren konnte gezeigt werden, dass Mx1 wahrscheinlich mit
Untereinheiten der Polymerase und dem Nukleoprotein interagiert, um die virale
Transkription zu inhibieren (242). Außerdem gibt es Hinweise, dass die Interaktion mit
zellulären Faktoren für die antivirale Aktivität von Mx1 von Bedeutung ist (43, 267).
E
9
Einleitung
Ein weiterer Faktor mit antiviraler Wirkung ist PKR. Diese Serin/Threonin-Kinase liegt
hauptsächlich im Zytoplasma assoziiert mit Ribosomen vor (181, 195). PKR wird durch
Autophosphorylierung aktiviert (235), ein Prozess, der unter anderem durch dsRNA-Bindung
ausgelöst wird (26, 185, 195). Im aktivierten Zustand katalysiert sie die intermolekulare
Phosphorylierung von verschiedenen Proteinsubstraten wie z.B. der α-Untereinheit des
eukaryotischen Translationsinitiationsfaktors 2α (eIF-2α) (195) und des Transkriptionsfaktorinhibitors IκB (123, 166). Die Phosphorylierung von eIF2α führt zur Inhibierung der
Proteinsynthese (194). Außerdem ist PKR an der Auslösung von Apoptose und an der
Aktivierung von NF-κB beteiligt (37, 106).
Die 2’-5’-Oligoadenylat-Synthetasen gehören einer Gruppe von Enzymen an, die durch IFN
induziert werden und in der Lage sind, 2’-5’-Oligoadenylate aus bis zu fünf
Adenosintriphosphaten zu synthetisieren (102, 188). Diese 2’-5’-Oligoadenylate aktivieren
spezifisch die zelluläre Endoribonuklease RNaseL, welche dann die Spaltung von zellulären
und viralen RNAs vermittelt. Dies führt zur Inhibierung der Proteinsynthese (27). Die
degradierte RNA kann auch andere zytoplasmatische PRRs, wie RIG-I oder MDA-5,
aktivieren und wiederum zur Induktion der IFN-Expression dienen (143).
2.1.5 Das aviäre angeborene Immunsystem
Im Gegensatz zu dem angeborenen Immunsystem der Säuger ist das aviäre Immunsystem
wenig untersucht. Allerdings hat die vollständige Sequenzierung des Hühnergenoms 2004
(77) die Identifizierung der für die Immunantwort im Huhn wichtigen Gene stark
beschleunigt. Die jeweiligen Funktionen der Gene sind jedoch bisher noch wenig untersucht.
2.1.5.1 Die Zellen des aviären angeborenen Immunsystems
Als Hauptbestandteile des angeborenen Immunsystems bei Vögeln gelten NK-Zellen,
Heterophile, Makrophagen und DCs.
Heterophile, die das Gegenstück zu den Neutrophilen der Säuger darstellen, gelten als erste
Barriere gegen eindringende Pathogene. Sie zeigen phagozytische Fähigkeiten, haben aber im
Gegensatz zu den Neutrophilen der Säuger keine Myeloperoxidase und ihre granulären
Komponenten scheinen sich von denen der Säuger zu unterscheiden (176). Nach Stimulation
mit LPS (Lipopolysaccharid) oder Terpentin kommt es zu einer vermehrten Einwanderung
von Heterophilen (73), die nach Aktivierung durch Zytokine zahlreiche proinflammatorische
Zytokine wie IL-1 (Interleukin-1), IL-6 und IL-8 produzieren (117, 118).
E
10
Einleitung
Als weiterer wichtiger Bestandteil der Zellen des aviären Immunsystems sind die
Makrophagen zu nennen. Ein wesentlicher Unterschied zu den Säugern besteht darin, dass
residente Makrophagen weder im Lungengewebe noch in der Bauchhöhle zu finden sind.
Deshalb nimmt man an, dass eine rasche Einwanderung dieser Phagozyten zum
Entzündungsort von großer Bedeutung für die Kontrolle von Pathogenen ist (237). Erste
Studien haben gezeigt, dass vor allem IL-1 (66, 107) und IL-6 (2, 213) als Antwort auf
inflammatorische Stimuli freigesetzt werden. Die Induktion der IL-1-, IL-6-, IL-18- und
Chemokingene scheint ein einzigartiges Muster zu sein, da es in Makrophagenkulturen
sowohl bei bakteriellen als auch bei viralen (170) und parasitischen Infektionen auftritt (33).
Phänotypische Studien haben gezeigt, dass NK-Zellen in adulten Hühnern hauptsächlich im
Epithel des Darms zu finden sind und nur ein geringer Teil in der Milz und im Blut, im
Gegensatz zum Menschen oder der Maus, bei denen 15% der lymphoiden Zellen in diesen
Geweben NK-Zellen darstellen. Obwohl mittlerweile viele Hühnerzytokine kloniert und
charakterisiert wurden, sind ihre Effekte auf NK-Zellen wenig bekannt. Es wurde allerdings
gezeigt, dass die orale Gabe von IFN-α die NK-Zellaktivität nach Infektion mit MDV
(Marek’s disease virus)-Infektion reduziert (92), wohingegen die IFN-γ-Behandlung von NKZellen in vitro die Aktivität erhöht (152).
Für DCs wurde gezeigt, dass sie in der Lage sind, Phagozytose und Makropinozytose
durchzuführen, was zu einer effektiven Antigenpräsentation beiträgt. Da Vögel keine säugerähnlichen Lymphknoten besitzen, sind noch weitere Studien nötig, um den Ort der
antigenpräsentierenden Zellen genau zu identifizieren. Obwohl es Hinweise gibt, dass die
Milz eine Rolle beim Aufbau der Immunantwort spielt, zumindest wenn Antigene intravenös
appliziert werden, scheint es bei lokaler Gabe der Antigene noch andere Orte für die
Initiierung der Immunantwort zu geben (78). Sehr frühe Arbeiten beschreiben das
Vorhandensein lymphoider Knotenstrukturen in der Lunge (167), deren Rolle aber noch nicht
näher untersucht wurde.
2.1.5.2 Die Interferone des Huhns
Das erste bekannte IFN, das vor ca. 50 Jahren entdeckt wurde, war das Hühner-IFN (88). Bis
heute wurden zwei Untergruppen der Typ I Interferone im Huhn identifiziert: IFN-α und IFNβ. Für beide wurde bereits gezeigt, dass sie antiviral wirken (204, 211), wobei die antivirale
Aktivität von IFN-β im Vergleich zum IFN-α um einen Faktor von ca. 20 niedriger ist. Wie
bei Säugern besteht die IFN-α-Familie aus mehreren intronlosen Genen, wohingegen nur ein
einziges intronloses IFN-β-Gen auf dem Z-Chromosom zu finden ist. Bis heute wurden 10
E
11
Einleitung
verschiedene IFN-α-Gene identifiziert, die sich ebenfalls auf dem Z-Chromosom befinden
(157, 211). Die Hühner Typ I Interferone weisen nur eine etwa 25%ige Sequenzhomologie zu
den entsprechenden Säuger-Interferonen auf (138). Sowohl IFN-α als auch IFN-β werden
nach viraler Infektion von Makrophagen und embryonalen Fibroblasten exprimiert (210), aber
nur IFN-α wird auch in der Niere und im Thymus nach oraler Stimulation mit synthetischen
RNA-Analoga exprimiert (236). Ähnlichkeiten bezüglich der Promotorstrukturen, der
Induzierbarkeit
und
der
Hitze-
und
Säurestabilität
deuten
trotz
der
großen
Sequenzunterschiede darauf hin, dass es sich bei den aviären Typ I Interferonen tatsächlich
um echte Homologe zu dem Säuger IFN-α beziehungsweise IFN-β handelt (218).
Das Hühner-IFN-γ wird in die Gruppe der Typ II Interferone eingeordnet und ist, wie das
Gegenstück der Säuger, hitze- und säurelabil und stimuliert typische IFN-γ-induzierbare Gene
wie das NO (Stickstoffmonoxid)-Synthetase-Gen oder das IRF-1-Gen. Die Hauptaufgabe ist
jedoch die Aktivierung von Makrophagen. Außerdem wurde gezeigt, dass es ebenfalls
antivirale Aktivität besitzt und für die Hochregulierung der MHC (major histocompatibility
complex) II-Expression verantwortlich ist (39, 218, 259). Hühner-IFN-α und IFN-γ scheinen
synergistisch zu wirken (205), was eine weitere Gemeinsamkeit zwischen dem Säuger- und
dem aviären Immunsystem darstellt.
Das erst kürzliche klonierte und charakterisierte IFN-λ wird zu den Typ III Interferonen
gezählt. Es enthält fünf exogene Regionen auf Chromosom 7 und weist eine 36%ige
Sequenzhomologie zu dem humanen IFN-λII auf. Genau wie die Typ I Interferone besitzt es
antivirale Eigenschaften (97).
2.1.5.3 Die Toll-like Rezeptoren im Huhn
Als erster Hühner-TLR wurde TLR2 entdeckt (17), gefolgt von TLR4 (130), TLR5 (182) und
TLR7 (140). Bis heute wurden noch weitere TLR-Gene gefunden, über deren Funktion
allerdings noch nicht viel bekannt ist. Im Folgenden soll nur auf diejenigen TLRs
eingegangen werden, die für eine virale Erkennung essentiell sind.
Der humane und der Hühner-TLR3 weisen eine 58%ige Aminosäuresequenzidentität auf und
werden beide in den meisten Geweben und Zellpopulation exprimiert (87). Behandlung von
Hühner-Milzzellen mit poly(I:C) führt wie im humanen System über TLR3 zu einer
Hochregulierung der mRNAs für IFN-α und IFN-β (182). Außerdem konnte gezeigt werden,
dass dieselbe Behandlung zur Produktion von NO in der Makrophagenzelllinie HD11 führt
(31).
E
12
Einleitung
Für TLR4 bei Säugern konnte gezeigt werden, dass nach LPS-Behandlung große Mengen
proinflammatorischer Zytokine, wie z.B. TNF-α (Tumor-Nekrosefaktor α) und IL-1β
sezerniert wurden. Hühner scheinen jedoch gegenüber der systemischen Behandlung mit LPS
relativ resistent zu sein (1) und nur auf sehr große Mengen zu reagieren (239). Der HühnerTLR4 weist 44% Homologie zu dem humanen TLR4 auf (130). In mehreren
Inzuchthühnerstämmen wurden verschiedene Sequenzpolymorphismen gefunden, die zu der
fehlenden Reaktion auf eine Stimulation mit LPS beitragen könnten (130). Der Hühner-TLR4
findet sich vor allem auf Makrophagen und Heterophilen (87, 130).
Die Stimulierung von Hühner-HD11-Zellen mit verschiedenen TLR7/8-Liganden ruft eine
starke Zytokinantwort hervor. Eine Hochregulierung der IL-1β-, IL6- und IL8-, jedoch nicht
der IFN-α- und IFN-β-mRNA-Level konnte gezeigt werden (182). Dieser Unterschied zum
Säuger-Immunsystem könnte für die Klärung der Frage, wie das aviäre angeborene
Immunsystem sich gegen eine Reihe von viralen Pathogenen schützt, sehr wichtig sein.
Obwohl gezeigt werden konnte, dass Hühner auf klassische TLR9-Liganden wie kurze
unmethylierte CpG-DNA reagieren (61, 137, 203, 263), wurde kein TLR9-Ortholog im Huhn
gefunden. Es wird angenommen, dass die Erkennung von CpG-Motiven über einen anderen
PRR läuft.
Die Aktivierung der verschiedenen TLRs beim Huhn führt zur Produktion verschiedener
Zytokine, Interferone und Chemokine. Verschiedene Studien konnten zeigen, dass die
generellen Elemente bei der TLR-Signalkette bei Säugern und Hühner konserviert sind (31,
116). Über die Rolle der TLRs bei der Erkennung von Influenza-A-Viren ist nichts Genaues
bekannt. Es wurde jedoch gezeigt, dass es nach Infektion mit Influenza-A-Viren zu einer
Hochregulation von TLR1, TLR3 und TLR7 kommt (97, 155, 189).
2.1.5.4 Interferon-induzierte Gene im Huhn
Da beim Huhn über die IFN-induzierten Gene noch nicht allzu viel bekannt ist, soll im
Folgenden nur auf das Hühner-Mx-Protein und auf die Proteinkinase PKR eingegangen
werden.
Beim Säuger wurde wie in Kapitel 2.1.4 beschrieben von mehreren Gruppen gezeigt, dass
sowohl das murine Mx1-Protein als auch das humane MxA-Protein antivirale Aktivität gegen
eine Reihe von Viren besitzen. Das Hühner-Mx-Gen besitzt ebenfalls einen durch IFN
induzierbaren Promotor und wird nach Virusinfektion induziert (202). Es konnte jedoch keine
antivirale Aktivität gegen z.B. Influenza-A-Viren, VSV (vesicular stomatitis virus), Thogotooder Sendai-Virus gezeigt werden (12). Dasselbe gilt für das Mx-Protein von Enten (7). Es
E
13
Einleitung
wurde gezeigt, dass das Hühner-Mx-Protein sich vor allem im Zytoplasma befindet und sehr
polymorph ist. Des Weiteren wurde spekuliert, dass ein Aminosäureaustausch an Position 631
von Serin zu Asparagin die antivirale Aktivität gegen Influenzaviren und VSV beeinflussen
könnte (111). Letzteres konnte aber in späteren Studien von verschiedenen Gruppen weder in
Zellkultur noch durch in vivo-Experimente bestätigt werden (11, 212). Man geht deshalb
davon aus, dass das Hühner-Mx-Protein keine antivirale Aktivität gegen Influenza-A-Viren
aufweist.
Die dsRNA-Bindedomäne von PKR weist eine hohe Konservierung zwischen verschiedenen
Spezies auf. Auch die Kinasedomäne weist zu anderen Spezies eine hohe Homologie auf, wie
z.B. 74% zum Menschen und 82% zur Maus. Funktionelle Untersuchungen bezüglich der
antiviralen Funktion der PKR im Huhn wurden bis heute kaum durchgeführt. Es wurde
lediglich gezeigt, dass 3T3-Zellen, die mit Hühner-PKR-cDNA transient transfiziert wurden,
resistent gegenüber Infektion mit VSV sind (110). Genauere Analysen und eine mögliche
Relevanz von aviärer PKR in vivo stehen allerdings noch aus.
2.2 Das Influenza-A-Virus
Influenzaviren gehören zur Familie der Orthomyxoviridae und werden aufgrund von
Unterschieden im Nukleo- und Matrixprotein in die Typen A, B und C unterteilt. Aviäre
Influenzaviren gehören dem Typ A an. Serologisch werden die Influenzaviren nach ihren
Oberflächenproteinen, dem Hämagglutinin (HA) und der Neuraminidase (NA) eingeteilt.
Derzeit unterscheidet man 16 HA-Subtypen und 9 NA-Subtypen (50, 254). Beim Menschen
verursachen Influenzaviren die klassische Virusgrippe, die eine fiebrige Erkrankung der
Atemwege darstellt. Der Tod tritt meist als Folge einer viralen Lungenentzündung oder einer
sekundären respiratorischen, bakteriellen Infektion ein. Das Auftreten von mindestens vier
Influenzapandemien im 19. Jahrhundert, drei im 20. Jahrhundert und einer im neuen
Jahrtausend mit insgesamt mehreren Millionen Todesfällen zeigt, dass es sich bei einer
Influenzavirus-Infektion um eine sehr verheerende, lebensbedrohliche Erkrankung handeln
kann (129). Vor allem die „spanische Grippe“ forderte 1918 weltweit nach allgemeinen
Schätzungen um die 50 Millionen Todesopfer (94, 240). Durch selektierte Punktmutationen
der Oberflächenglykoproteine HA und NA treten alle 1-2 Jahre neue epidemische InfluenzaA-Stämme auf. Diese kleinen Veränderungen nennt man antigenic drift. Sie führen dazu, dass
keine anhaltende Immunität gegen das Virus besteht, weder nach einer natürlichen Infektion
noch nach einer Impfung. Die Pandemie von 1918 wurde durch ein H1N1-Virus verursacht,
E
14
Einleitung
das offenbar von Vögeln abstammte (190). Die Ursache der nachfolgenden Pandemien waren
reassortante Viren, die drei (1957) beziehungsweise zwei Segmente (1968) von aviären
Influenzaviren enthielten (101). Die Bildung von Reassortanten bei Infektion eines Wirtes mit
unterschiedlichen Virussubtypen bezeichnet man als antigenic shift.
2.2.1 Partikel- und Genomstruktur der Influenza-A-Viren
Influenza-A-Viren sind pleomorphe, behüllte Partikel mit einem durchschnittlichen
Durchmesser von 120 nm. Sie besitzen ein einzelsträngiges, segmentiertes RNA-Genom in
negativer Orientierung (Abbildung 2.4 A). Die 8 Segmente werden vollständig von
Nukleoproteinen (NP) komplexiert (29, 141) und bilden zusammen mit dem assoziierten
Polymerasekomplex, der aus den Untereinheiten PB1 (polymerase basic protein 1), PB2
(polymerase basic protein 2) und PA (polymerase acidic protein) besteht die so genannten
Ribonukleoproteine (RNPs) (Abbildung 2.4 B). NP ist unter anderem beim Transport der
RNPs in den Kern (148) und bei der Replikation und Transkription (121, 248) beteiligt. An
den 5’- und 3’-Enden der Segmente befinden sich so genannte non coding regions (NCRs),
die regulatorische Sequenzen wie das Verpackungssignal und die Promotorregion enthalten
(109).
In
die
von
der
Wirtsmembran
stammenden
Lipidhülle
sind
die
glykosylierten
Oberflächenproteine HA und NA eingelagert. HA liegt als Trimer vor und ist für die
Adsorption der Viruspartikel an die Neuraminsäuren auf der Wirtszelle und die
Membranfusion nach der rezeptorvermittelten Endozytose verantwortlich. NA dagegen liegt
als Tetramer vor und spielt bei der Freisetzung der Partikel und bei der Verhinderung der
Bildung von Virusaggregaten eine entscheidende Rolle. Die Verbindung der Neuraminsäure
zur benachbarten Galaktose (entweder α2-3 oder α2-6) bestimmt die Wirtsspezifität (76).
Aviäre Influenza-A-Viren weisen generell eine höhere Affinität zu α2-3 gebundener
Neuraminsäure auf. Diese ist auch der dominierende Rezeptortyp in epithelialen Geweben
endodermaler Herkunft (Darm, Lunge) bei Vögeln (56, 105). Humane Influenza-A-Viren
erkennen dagegen Neuraminsäure, die in α2-6-Bindungen an Galaktose verknüpft ist. Dieser
Rezeptor kommt am häufigsten auf Epithelzellen des oberen Respirationstraktes des
Menschen vor. Diese Rezeptor-Präferenzen sind unter anderem dafür verantwortlich, dass
aviäre Viren nicht ohne weiteres auf den Menschen übertragen werden können (224, 225).
Allerdings ist auch gezeigt worden, dass es in der Trachea des Menschen zilientragenden
Zellen gibt, die auch „aviäre Rezeptoren“ tragen (149). Außerdem besitzen Hühnerzellen auch
einige wenige „humane Rezeptoren“ (105), so dass der Mensch nicht vollständig resistent
E
15
Einleitung
gegenüber den aviären Influenza-A-Viren ist und umgekehrt (9). Bei Schweinen und bei
Wachteln kommen beide Rezeptoren häufiger vor, so dass diese beiden Spezies als mögliche
Quellen von Reassortanten gelten (89, 104, 175, 177, 249).
Ein weiteres Protein der Hüllmembran ist das M2 (Matrixprotein 2)-Protein, das als H+Ionenkanal fungiert, um nach erfolgter rezeptorvermittelter Endozytose das Innere der
Viruspartikel anzusäuern. Dadurch wird die Interaktion des Matrixproteins M1 mit den RNPs
aufgehoben. Nach erfolgter Fusion der Virusmembran mit der Endosomenmembran werden
die RNPs freigesetzt. Das M1-Protein ist mit der Innenseite der Hüllmembran assoziiert und
spielt eine Rolle bei der Verpackung der RNPs und bei der Freisetzung der Partikel (budding).
Das kleinste Segment (Segment 8) kodiert für das Nichtstruktur-Protein 1 (NS1) und das
NEP-Protein (nuclear export protein), das von derselben RNA durch alternatives Spleißen
synthetisiert wird (86, 127). Das NEP-Protein ist wichtig für den Export neu gebildeter
vRNPs aus dem Kern in das Zytoplasma (165). Das NS1-Protein ist ein multifunktionelles
Protein, auf dessen Eigenschaften im Detail noch in Kapitel 2.2.5 eingegangen wird.
Auf dem 2. Segment ist durch einen alternativen offenen Leserahmen neben dem PB2-Protein
noch ein weiteres Protein kodiert, das Nichtstruktur-Protein PB1-F2. Dieses ist in den
Mitochondrien von Zellen lokalisiert, die mit Influenzaviren infiziert wurden und trägt zur
Apoptose der Zellen bei (22, 265). Außerdem wurde gezeigt, dass es spezifisch alveolare
Makrophagen zerstört, wodurch die Etablierung einer bakteriellen Pneumonie erleichtert wird
(22).
A
B
HA
NEP
NA
M1
M2
NP
PA
PB2 PB1
PA
HA
NP
NA M
NS
C
PB2
ss(-)RNA-Segmente
PB1
Abbildung 2.4: Aufbau des Influenza-A-Viruspartikels
(A) Schematische Darstellung eines Partikels. (B) Schematische Darstellung eines viralen Ribonukleoproteinkomplexes,
bestehend aus einem einzelsträngigen RNA-Gensegment (vRNA), dem Nukleoprotein und den Polymeraseuntereinheiten
PB1, PB2 und PA. (C) Elektronenmikroskopische Aufnahme freigesetzter Viruspartikel (164).
E
16
Einleitung
Die Replikation und Transkription der Influenzaviren finden im Zellkern mit Hilfe des RNPassoziierten Polymerasekomplexes statt. Nach erfolgter Translation werden die neu
synthetisierten Proteine zur Plasmamembran transportiert. Zusammen mit den viralen RNPs
werden die Viruspartikel durch einen als budding bezeichneten Prozess von der Membran
freigesetzt. Die Zeit vom Eintritt in die Zelle bis zur Produktion neuer Viren beträgt im
Durchschnitt 6 Stunden. (Abbildung 2.5 gibt einen Überblick über den Replikationszyklus der
Influenza-A-Viren.)
Endosom
HA
NA
M2
Transkription
Replikation
Golgi
ER
mRNA
M1
PB1-F2
PA
PB1
PB2
NP
NS1
M1
NEP
mRNA
Abbildung 2.5: Schema des Replikationszyklus der Influenza-A-Viren
Nach der rezeptorvermittelten Endozytose werden die vRNP-Komplexe in das Zytoplasma freigesetzt und sofort in den
Zellkern transportiert, in der die Replikation und Transkription stattfinden. Die mRNAs werden für die Translation in das
Zytoplasma transportiert. Die frühen viralen Proteine, d.h. diejenigen, die für die Replikation und Transkription benötigt
werden, werden zurück in den Kern transportiert. M1 und NEP erleichtern zu späteren Zeitpunkten den Kernexport neu
synthetisierter vRNPs. PB1-F2 assoziiert mit den Mitochondrien. Der Zusammenbau und der Budding-Prozess finden an der
Plasmamembran statt [verändert nach (160)].
2.2.5 Das NS1-Protein der Influenza-A-Viren
Das NS1-Protein ist ein für die Virusvermehrung nicht essentieller Virulenzfaktor, der viele
verschiedene akzessorische Funktionen während der Infektion hat. Die Hauptfunktion von
NS1 ist es, der virusinduzierten IFN-α/β-Immunantwort entgegen zu wirken beziehungsweise
diese zu inhibieren. NS1 ist auf einer kolinearen mRNA kodiert, die von der vRNA des 8.
Segments transkribiert wird.
Die Länge von NS1 hängt vom Virusstamm ab und beträgt zwischen 230 und 237
Aminosäuren. Aufgrund phylogenetischer Analysen werden NS1-Proteine in zwei große
Gruppen eingeteilt: Allel A und Allel B (139, 238). Die NS1-Proteine von Influenza-A-Viren
von Schweinen und Pferden und einigen aviären werden als Allel A eingeordnet, die von allen
E
17
Einleitung
restlichen aviären Viren werden als Allel B eingeordnet. Alle NS1-Proteine besitzen eine Nterminale RNA-Bindungsdomäne (Aminosäuren 1-73), von der gezeigt wurde, dass sie
in vitro RNA sequenzunabhängig mit einer geringen Affinität binden kann (25, 74). Cterminal besitzt NS1 eine Effektordomäne, die zum einen Interaktionen mit verschiedenen
Proteinen der Wirtszelle vermittelt, zum anderen die RNA-Bindungsdomäne stabilisiert (251)
(Abbildung 2.6).
Effektor-Domäne
RNA-Bindungsdomäne
1
73
230
NLS
34-38
30
NLS
216-221
NES
137-146
50
RNA-Bindung
81-113
123-127
103, 106, 144-188
223-230
eIF4G-Bindung
PKR-Bindung
CPSFBindung
PABIIBindung
Abbildung 2.6: Schematische Darstellung der funktionellen Domänen des NS1-Proteins
Die RNA-Bindungsdomäne umfasst die ersten 73 Aminosäuren am N-Terminus, die restlichen Aminosäuren am C-Terminus
bestehen aus der Effektordomäne. Die Positionen einiger Interaktionspartner von NS1 sind dargestellt.
Bis vor kurzem wurde angenommen, dass das NS1-Protein als Homodimer in der Zelle
vorkommt, wobei beide Domänen an der Dimerisierung beteiligt sind (159). Neuere
Röntgenstrukturanalysen zeigten jedoch, dass es vielmehr zu der Bildung von Ketten kommt,
die aus mehreren NS1-Molekülen bestehen, und dass je drei dieser Ketten eine tubuläre
Struktur ausbilden, in der die RNA gebunden werden kann (15) (Abbildung 2.7).
A
B
C
Abbildung 2.7: Struktur des NS1-Proteins (H5N1)
(A) Tubuläre Struktur von NS1 mit dem 20 Å-weiten Tunnel. Jede der drei Ketten ist in einer anderen Farbe dargesetllt. (B)
Oberflächendarstellung der tubulären Struktur. Jede Kette ist in einer anderen Farbe dargestellt. (C)
Kryoelektronenmikroskopische Aufnahme eines nativen H5N1-NS1 in Anweseneheit von dsRNA (15).
E
18
Einleitung
In virusinfizierten Zellen befinden sich die NS1-Proteine hauptsächlich im Nukleus, zu
späteren Zeitpunkten aber auch im Zytoplasma (64, 162). Abhängig vom Virusstamm besitzt
es ein oder zwei nuclear localisation signals (64), die den Import über Importin-α vermitteln
(151). Des Weiteren wurde gezeigt, dass NS1 in der Lage ist, durch Bindung an
beziehungsweise Rekrutierung von verschiedenen zellulären Faktoren, z.B. eIF4GI
(eukaryotischer Translationsinitiationsfaktor 4GI) (4) und PABPI (poly A binding protein 1)
(18) die virale Translation zu verstärken.
Eine wichtige Funktion von NS1 ist dessen Einfluss auf das angeborene Immunsystem. Hier
gibt es virusstammabhängige Unterschiede in der Ausübung der Funktion. Für den InfluenzaStamm A/Udorn/72 wurde gezeigt, dass das NS1-Protein in der Lage ist, die Prozessierung
zellulärer mRNAs zu inhibieren und damit deren Export zu unterbinden (169). Dazu bindet
NS1 sowohl an die 30 kDa-Untereinheit von CPSF (cleavage and polyadenylation specificity
factor) (158, 163), als auch an PABPII (23). Da die Polyadenylierung viraler RNAs
unabhängig von den zellulären Prozessierungsfaktoren ist (169), sind die viralen RNAs von
dem generellen shutdown, der auch Gene des IFN-Signalwegs beinhaltet, nicht betroffen.
Außerdem scheinen NS1-Proteine von anderen Influenza-A-Stämmen in der Lage zu sein,
den Export zellulärer, polyadenylierter mRNAs aus dem Zellkern zu inhibieren (49, 186). Es
gibt jedoch auch Influenza-Stämme, wie z.B. A/Puerto Rico/8/34 (PR8), deren NS1 nicht in
der Lage ist, an CPSF zu binden und die andere Strategien entwickelt haben, um die IFNProduktion zu inhibieren. Es wurde von mehreren Gruppen gezeigt, dass NS1 von PR8 einen
Komplex mit RIG-I bildet und dadurch die RIG-I/IPS-1-Signalkaskade wirkungsvoll
inhibiert. (154, 168, 183). Später wurde deutlich, dass für eine maximale IFN-Produktion
nach einer Virusinfektion die Ubiquitinylierung von RIG-I durch die Ubiquitinligase TRIM25
wichtig ist (55), und dass NS1 in der Lage ist, direkt an TRIM25 zu binden und damit die
IFN-Produktion zu inhibieren (54).
Überdies verhindert NS1 die Aktivierung von PKR, die normalerweise nach Aktivierung
durch virale RNA zelluläre Transkriptionfaktoren phosphoryliert und dadurch die zelluläre
und virale Proteinsynthese inhibiert (60). Für Influenza-B-Viren wurde erst kürzlich gezeigt,
dass der Export von vRNPs aus dem Kern in das Zytoplasma zu einer Aktivierung von PKR
führt. Das NS1-Protein des Influenza-B-Virus ist in der Lage, einen Komplex mit PKR zu
bilden, dessen Bindung durch die Anwesenheit von RNA erleichtert wird (34).
E
19
Einleitung
Influenza-A-Virus
NS1
dsR
N
ds
R
A
TRIM25 RIG-I
dsRNA
NA
NS1
dsRNA
b
PKR
a
NS1
PACT
NF-κB
IRF3
NS1
2‘-5‘ OAS
b
P
eIF2α
2‘5‘(A)n
2‘5‘(A)n
AAAAA
AAAAA
5‘Cap
5‘Cap
RNase L
d
AAAAA
NS1
c
PABPII
CPSF30
NS1
eIF4GI
PABI
Prä-mRNA
5‘Cap
3‘
Zellkern
Abbildung 2.8: Schematische Darstellung der NS1-Funktionen innerhalb der Zelle
(a) Prätranskriptionelle Limitierung der IFN-β-Induktion. (b) Inhibierung der antiviralen Eigenschaften von PKR und
OAS/RNaseL. (c) Posttranskriptioneller Block der Prozessierung und des Kernexports aller zellulären mRNAs. (d)
Verstärkung der viralen mRNA-Translation.
Verschiedene Studien konnten belegen, dass NS1 Einfluss auf die Antwort des
Immunsystems ausübt. So konnte z.B. im Mausmodell gezeigt werden, dass das NS1-Protein
eines humanen H5N1-Influenza-Stammes die Expression von proinflammatorischen
Zytokinen in der Lunge und im Blut reduziert (84). Andererseits wurde beschrieben, dass
Viren, die das NS1-Gen hoch pathogener H5N1-Stämme von 1997 tragen, besonders stark
proinflammatorische Zytokine wie TNF-α induzieren (24). Ein Glutamatsäurerest an Position
92 soll für die Resistenz gegen die durch IFN und TNF-α hervorgerufenen antiviralen Effekte
im Schwein verantwortlich sein (206).
Viren, die aufgrund von Mutationen oder Deletionen im NS1-ORF (open reading frame) nicht
in der Lage sind, ein Volllängen-NS1-Protein zu exprimieren, können nur in Zellen oder
Mäusen mit defektem angeborenen Immunsystem replizieren (59, 114). Diese Viren sind in
der Lage, eine starke IFN-Antwort zu induzieren, wobei diese Fähigkeit in vivo stark von der
Replikationsfähigkeit abzuhängen scheint (115).
Unabhängig von den Auswirkungen auf das IFN-System scheint NS1 mit dem viralen
Polymerase-Komplex zu assoziieren (124, 147) und auch die virale Replikation zu
beeinflussen (45). Des Weiteren kann NS1 auch den zellulären Phosphatidylinositol-3-
E
20
Einleitung
Kinase/Akt-Signalweg aktivieren und dadurch die virale Replikation beeinflussen (41, 67,
209).
2.2.3 Aviäre Influenza-A-Viren
Das natürliche Reservoir von Influenza-A-Viren bilden Wasservögel, insbesondere der
Ordnungen Anseriformes (Enten, Gänse und Schwäne) und Charadriiformes (Möwen und
Watvögel). In diesen Vögeln verläuft die Replikation hauptsächlich intestinal, das Virus wird
meist fäkal-oral übertragen und die Infektion ist asymptomatisch (258). Wahrscheinlich sind
die meisten Vogelarten für Influenzaviren empfänglich, jedoch gelten Hühnervögel als
besonders anfällig (51, 120, 254). Zumeist weisen die Influenzaviren eine geringe
Pathogenität auf und befinden sich mit ihrem Wirt in einem natürlichen Gleichgewicht (63,
234). Solche LPAIV (low pathogenic avian influenza virus) können auf Hühner und andere
Geflügelarten übertragen werden und in diesen milde Krankheitssymptome auslösen. Es gibt
allerdings auch Influenza-Stämme, die das Potenzial haben durch Mutationen höhere
Pathogenität zu erlangen. Charakteristisch für diese HPAIV (highly pathogenic avian
influenza virus) ist eine multibasische Spaltstelle im Hämagglutinin, die durch ubiquitär
vorhandene Furin-ähnliche Proteasen gespalten werden kann. Dadurch ist das Virus in der
Lage, zusätzlich zu den üblichen Replikationsorten, den Epithelzellen des oberen
Respirations- und des Intestinaltraktes, in anderen Geweben zu replizieren und sich
systemisch auszubreiten (81, 222, 257). Diese hoch pathogene aviäre Influenza wurde
erstmals im Jahre 1878 als infektiöse Erkrankung bei Hühnern in Italien beschrieben (96).
Aber erst 1955 wurde das für die Krankheit verantwortliche Agens als Influenza-A-Virus
identifiziert und charakterisiert (198). Heutzutage sind vor allem Viren der Subtypen H5 und
H7 als hoch pathogen bekannt. Die auftretenden Mutationen wurden meist nicht in dem
eigentlichen Reservoir, den Wasservögeln, sondern im domestizierten Geflügel beobachtet
(253). Diese HPAIV werden dann innerhalb des Geflügelbestandes übertragen, bei Kontakt
aber auch auf Wasservögel. Diese zeigen dann abhängig von der Art und dem Alter des
Vogels, sowie des Virusstamms ein abweichendes Krankheitsbild. Allerdings waren vor dem
Auftreten der asiatischen H5N1-Viren Übertragungen auf Wasservögel eher selten (229).
Zwischen 2003 und 2007 gab es in mehr als 20 Ländern in Asien, Afrika und Europa Fälle
von aviärer Influenza bei Tieren und mehr als 1,5 Millionen Vögel wurden gekeult, um eine
Ausbreitung des Virus zu verhindern (35). Bis 2009 registrierte die WHO 424 humane Fälle
und 261 Todesfälle (160). Im Gegensatz zu saisonalen Influenza-A-Viren scheint dieser
aviäre H5N1-Stamm bevorzugt junge Erwachsene und Kinder zu infizieren. Allerdings gab es
E
21
Einleitung
kaum Fälle einer Mensch-zu-Mensch-Übertragung, außer bei sehr nahem Kontakt zu
infizierten Personen (35).
2.2.4 Die Übertragung von Influenza-A-Viren
Die Übertragung der Influenza-A-Viren auf dem direkten Weg von Vogel zu Vogel findet
hauptsächlich auf dem fäkal-oralen Weg statt (258). Es gibt aber auch indirekte
Übertragungswege über kontaminiertes Wasser und verschiedene Gegenstände. Das Risiko,
dass die Viren auf domestiziertes Geflügel übertragen werden ist bei Freilandhaltung am
größten, wenn Wasser oder Futter von Wildvögeln kontaminiert werden können (19, 75). Die
Hühnervögel werden durch den direkten Kontakt mit virushaltigen Exkrementen oder
anderem Material infiziert. Sobald sich das Virus erst einmal an den neuen Wirt adaptiert hat,
kommt es zu horizontalen Übertragungen innerhalb des Bestandes.
Die Übertragung von aviären Influenzaviren auf den Menschen stellt eher ein seltenes
Ereignis dar. Nur bei sehr engem Kontakt zu lebendem Geflügel oder bei Kontakt zu
Gegenständen, die mit dem Kot infizierter Tiere beschmutzt sind, kann es zu einer Infektion
kommen. Die Übertragung von Mensch zu Mensch findet hauptsächlich durch Tröpfchen aus
der Nase oder dem Rachen einer infizierten Person statt. Sie kann auch durch direkten
Hautkontakt oder durch indirekten Kontakt mit Sekreten aus den Atemwegen stattfinden (96).
2.3 Das Krankheitsbild beim Huhn
Bei einer Infektion von Hühnervögeln mit LPAIV treten milde Symptome wie gesträubtes
Gefieder, vorübergehender Abfall der Legeleistung oder Gewichtsverlust, aber auch leichte
respiratorische Erkrankungen auf (20, 226). Der initiale Replikationsort ist die Nasenhöhle,
von wo aus sich das Virus in den oberen Respirations- und den Intestinaltrakt ausbreitet (227,
228, 230).
Bei HPAIV wird ebenfalls zuerst die Nasenhöhle infiziert. Allerdings sind diese Viren in der
Lage, sich systemisch durch Infektion der vaskulären Endothelien, aber auch von
Immunzellen auszubreiten (226). Dadurch kommt es zu schwerwiegenden Symptomen und
die Mortalität beträgt oft 100% (229). Ein Teil der infizierten Tiere zeigt schwere Apathien
und Bewegungslosigkeit (125), bei anderen treten Ödeme in den federfreien Teilen des
Kopfes, Zyanosen des Kammes, Kehllappens und der Beine, sowie schwere Atmung auf. Bei
Hennen setzt die Legetätigkeit am Ende völlig aus (42, 226). Oftmals werden die Tiere tot
aufgefunden, bevor klinische Symtpome aufgetreten sind (226). Bei Eintritt des Todes
E
22
Einleitung
innerhalb von 24-36 Stunden nach Infektion oder bei akuten Verläufen gibt es meist keine
charakteristischen,
makroskopischen
Veränderungen
der
Organe
(178).
Die
verschiedenartigen Läsionen zusammen mit viralem Antigen können in unterschiedlichen
Organen im gesamten Körper detektiert werden (156). Nach der systemischen Ausbreitung
findet man die Viren unter anderem im Myokard, der Milz, den Nebennieren, der
Bauchspeicheldrüse und im Gehirn. Die Aktivierung von Endothelien und Leukozyten kann
zu einer systemischen und unkoordinierten Zytokinfreisetzung führen, was oft ein MultiOrganversagen zur Folge hat (46, 108). Bei weniger empfänglichen Arten wie Enten und
Gänsen überwiegen nach Infektion mit HPAIV nervöse Symptome, ungewöhnliche
Haltungen und unkoordinierte Bewegungen, aber es sind kaum Todesfälle beobachtet worden
(96, 226).
2.4 Zielsetzung der Arbeit
Das für die Pandemie im Jahr 1918 verantwortliche H1N1-Influenza-A-Virus war aviären
Ursprungs und ist nach Mutation auf den Menschen übergegangen (94, 240). Auch die Viren
der nachfolgenden Pandemien besaßen aviäre Segmente. Dies zeigt sehr deutlich, wie wichtig
es ist, aviäre Viren in ihrem natürlichen Wirt zu untersuchen, um in Zukunft sichere und
effiziente Vakzine für Geflügel herstellen oder resistente Hühnerlinien entwickeln zu können.
Ökonomische Gründe spielen ebenfalls eine große Rolle, da Ausbrüche von hoch pathogener
aviärer Influenza katastrophale Folgen für die Geflügelwirtschaft und auch für die
Ernährungssituation in vielen Entwicklungsländern haben.
Es wurde gezeigt, dass die frühe Immunantwort wichtig für die Schwere und den Ausgang der
Erkrankung von Infektion mit aviären Influenza-A-Viren in Mäusen und Makaken ist (98,
112). Im Gegenzug dazu ist wenig bekannt über die frühe Immunantwort und wichtige
Wirtsfaktoren, die eine Rolle bei der Induktionsphase der Immunantwort im Huhn spielen.
Obwohl viele Zytokine des Huhns mittlerweile identifiziert wurden (95), ist die Kinetik der
Zytokininduktion im Huhn nach Virusinfektion und der Einfluss der Zytokine auf den
Ausgang
der
Erkrankung
wenig
erforscht.
Aufgrund
der
Verfügbarkeit
vieler
Inzuchtmausstämme und knockout-Mäuse weiß man bereits viel über das angeborene
Immunsystem der Maus. Solche Modellsysteme und Techniken sind für das aviäre System
nicht vorhanden. Durch verschiedene in vitro-Modelle können zwei wichtige Mechanismen Infektion und Abwehr - untersucht werden. Um aber das Zusammenwirken von aviären
Influenzaviren mit dem aviären Immunsystem zu charakterisieren, ist es wichtig, HPAIV in
E
23
Einleitung
ihrem natürlichen Wirt zu untersuchen. In dieser Arbeit wurden dazu die aviären
Influenzavirusstämme
A/seal/Mass/1/1980
(H7N7)
und
A/cygnus
cygnus/Ruegen-
Germany/R65/2006 (H5N1) verwendet. Die Viren, die das Volllängen-NS1 exprimieren
sollten normalerweise in der Lage sein, die IFN-α/β-Produktion zu inhibieren. Deshalb wurde
zusätzlich zu den wild-type (wt)-Viren Mutanten hergestellt, die C-terminale Verkürzungen
im NS1-Protein aufweisen, sowie Mutanten, bei denen das NS1-Gen komplett deletiert
wurde. Diese Viren sollten anschließend in verschiedenen aviären Systemen, im Vergleich
aber auch in der Maus, in vitro und in vivo untersucht werden, um die Interaktion von NS1
mit dem aviären angeborenen Immunsystem besser verstehen zu können.
E
24
Material und Methoden
3. Material und Methoden
3.1 Chemikalien
Chemikalien wurden von den Firmen Sigma (Deisenhofen), Invitrogen (Karlsruhe), Merck
(Darmstadt), Amersham Pharmacia Biotech (Freiburg), Roth (Karlsruhe), Serva (Heidelberg),
Eppendorf (Hamburg) verwendet. Gängige Laborchemikalien wurden, wenn nicht anders
aufgeführt, im Reinheitsgrad p.a. verwendet.
Chemikalie
Firma
Aceton
Acrylamidlösung (30% mit 0,8% Bisaceylamid)
Agarose
Ammoniumpersulfat (APS)
Ampicillin
Avicel®
BactoTM Agar
BactoTM Trypton
BactoTM Pepton
Bovines Serum-Albumin (BSA)
Bradford Reagenz
Bromphenolblau
Dithiothreitol (DTT)
Essigsäure
Ethanol (absolut)
Ethidiumbromid
Ethylendiamintetraessigsäure (EDTA)
Ficoll
Formaldehyd
Formamid
Glucose
Glycerin
Guanidiniumhydrochlorid
Harnstoff
HCl
IPTG
Isopropanol
KCl
KH2PO4
Kristallviolett (C25H30CIN3)
β-Mercaptoethanol
Methanol
MgCl2
MgSO4
MOPS
Mowiol
Roth, Karlsruhe
Roth, Karlsruhe
Gibco BRL, Wiesbaden
Sigma, Deisenhofen
Bayer, Leverkusen
FMC BioPolymer, Belgien
BD Bioscience, Frankreich
BD Bioscience, Frankreich
BD Bioscience, Frankreich
Sigma, Deisenhofen
BioRad, München
Sigma, Deisenhofen
Sigma, Deisenhofen
Roth, Karlsruhe
Merck, Darmstadt
Sigma, Deisenhofen
Roth, Karlsruhe
Roth, Karlsruhe
Riedel de Haen, Seelze
Fluka, Neu-Ulm
Roth, Karlsruhe
Roth, Karlsruhe
Roth, Karlsruhe
Roth, Karlsruhe
Merck, Darmstadt
Boehringer, Mannheim
Merck, Darmstadt
Merck, Darmstadt
Merck, Darmstadt
Merck, Darmstadt
Roth, Karlsruhe
Roth, Karlsruhe
Roth, Karlsruhe
Roth, Karlsruhe
Roth, Karlsruhe
Sigma, Steinheim
E
25
NaCl
Na2HPO4
NaOAc
NaOH
Natriumdeoxycholat
Nickel-NTA Agarose
Nonidet P-40 (NP40)
Paraformaldehyd
peqGold TriFasTM
Phenol
Pipes
Polyvinylpyrrolidon
β-Propiolactone
RNA later
SlimFast
Sodium-Dodecyl-Sulfat (SDS)
TEMED
Tris
Triton X-100
Trizma® Base
TrueBlue™
Tween 20
Tween 80
Xylencyanol F
Material und Methoden
Roth, Karlsruhe
Merck, Darmstadt
Merck, Darmstadt
Roth, Karlsruhe
Merck, Darmstadt
Qiagen, Hilden
Calbiochem, USA
Merck, Darmstadt
peqLab, Erlangen
Fluka, Neu-Ulm
Fluka, Neu-Ulm
Roth, Karlsruhe
Acros Organics, USA
Qiagen, Hilden
Slim Fast, Wiesbaden
Roth, Karlsruhe
Fluka, Neu-Ulm
USB, USA
Fluka, Neu-Ulm
Sigma, Deisenhofen
KPL, USA
Merck. Darmstadt
Calbiochem, Canada
Sigma, Deisenhofen
Tabelle 3.1: Verwendete Chemikalien
3.2 Proteinmethoden
Chemikalie
Firma
ECL Western-Blot Detektionsreagenz
Immobilion-P-Transfer Membran
Naßblot-System PROTEAN II
Proteingelkammer PROTEAN II
Whatman-Papier
Amersham Bioscience, Freiburg
Millipore, Schwalbach
Biorad, München
Biorad, München
Whatman, Dassel
Tabelle 3.2: Verwendete Materialien für Proteinmethoden
3.3 Zellkulturmaterial
Material
Firma
DMEM high glucose
Fötales Kälberserum (FKS)
Hepes
Hühner-Serum
Medium 199 Hanks’
Optimem
Invitrogen, Karlsruhe
PAA Laboratories GmbH, Österreich
Life Technologies, Wiesbaden
Roth, Karlsruhe
Biochrom AG, Berlin
Gibco BRL, Wiesbaden
E
26
Penicillin/Streptomycin
Trypsin-Versen-Lösung
Material und Methoden
Gibco BRL, Wiesbaden
Life Technologies, Wiesbaden
Tabelle 3.3: Verwendetes Zellkulturmaterial
3.4 Transfektionsreagenzien
Reagenz
Firma
Lipofectamine™ 2000
Nanofectin
Invitrogen, Karlsruhe
PAA Laboratories GmbH, USA
Tabelle 3.4: Verwendete Transfektionsreagenzien
3.5 Sonstige Materialien
Material
Firma
Gewebekulturplatten
1,5 ml/2 ml Eppendorf-Röhrchen
15-, 50-ml Falcon-Gefäße
Immobilon®-P Transer-Membran
Luminometer-Röhrchen
Nytran-N (Nylon Transfer Membran)
PD-10-Säule
Sephadex G-50
Transfektionsröhrchen
Zellkulturflaschen
Greiner Bio-One GmbH, Frickenhausen
Eppendorf, Hamburg
BD Labware, Frankreich
Millipore, USA
Sarstedt, Nürnbrecht
Schleicher & Schuell, Dassel
Amersham Bioscience, Freiburg
Amersham Bioscience, Freiburg
BD Bioscience, Frankreich
Corning Inc., USA
Tabelle 3.5: Sonstige Materialien
3.6 Geräte
1
Gerät
Name
Firma
Bildaufnahmeprogramm
Bilddokumentationssystem
CO2-Inkubator
Heizblock
Hybridisierungsofen
Luminometer
Magnetrührer
PCR-Cycler
pH-Meter
Pipetten
Pipettierhilfe
Real Time Thermocycler
Quantity One Software
ChemiDoc
Heraeus 6000
Thermomixer compact
OV1
Sirius
RCT basic
Primus 25
766 Calimatic
Pipetmann® (P10-P1000)
Pipetus®-akku
7900 Real-time PCR System
BioRad, München
BioRad, München
Heraeus, Hanau
Eppendorf, Hamburg
Biometra Göttingen
Berthold, Bad Wildbad
IKA Labortechnik, Staufen
peqab, Erlangen
Knick, Berlin
Gilson, USA
Hirschmann, Eberstadt
Applied Biosystems
E
27
Schüttelwasserbad
Horizontalschüttler
Spektralphotometer
Tisch-Zentrifuge
Überkopfschüttler
Vakuumzentrifuge
Waage
Zellhomogenisator
Zellhomogenisator
Zentrifuge
Zentrifuge
Bakterienschüttler
GFL1083
KS 250 basic
NanoDrop®-ND-1000
Centrifuge 5424
Reax2
Hetovac VR-I
PM200
FastPrep®-24
TissueLyser II
Megafuge 1.0R
Sorvall RC-5B
Certomat® BS-1
Material und Methoden
GFL, Burgwedel
IKA Labortechnik, Staufen
Nanodrop Technologies, USA
Eppendorf, Hamburg
Heidolph, Kehlheim
Heto Lab Equipment, Dänemark
Mettler, Giessen
MP Biomedicals, Mannheim
Qiagen, Hilden
Heraeus, Hanau
DuPont Instruments, Bad Homburg
B.Braun Biotech, Meldingen
Tabelle 3.6: Verwendete Geräte
3.7 Enzyme und Größenstandards
Restriktionsenzyme wurden von Fermentas verwendet. Alle anderen Enzyme und
Größenstandards sind im Folgenden aufgeführt:
Material
Firma
Benzonase
DNase I
Gene RulerTM 1kb DNA Ladder
Gene RulerTM 100 bp DNA Ladder Plus
Herculase II Fusion Enzyme
Prestained SDS-PAGE Standard (low range)
RevertAidTM H Minus M-MuLV Reverse Transcriptase
Shrimp alkaline Phosphatase (SAP)
T4 DNA-Ligase
Taq Polymerase
Merck, Darmstadt
Fermentas, St-Leon-Rot
Fermentas, St-Leon-Rot
Fermentas, St-Leon-Rot
Stratagene, USA
Biorad, München
Fermentas, St-Leon-Rot
Roche, Mannheim
Eppendorf, Hamburg
Fermentas, St-Leon-Rot
Tabelle 3.7: Verwendete Enzyme und Größenstandards
E
28
Material und Methoden
3.8 Kit-Systeme
Kit
Firma
ECL plus Western Blotting Detection System
E.Z.N.A.® Gel Extraction Kit (Classic-Line)
ID VET AIV Screen ELISA
IFN-β-ELISA
ID Screen® Influenza A Antibody Competition ELISA kit
NucleoBond® PC100 Kit
pcDNA3.1/V5-His© TOPO® TA Expression Kit
Prime-It® II-Random Primer Labelling Kit
QuantiTect Probe RT-PCR Kit
Rapid DNA Ligation Kit
RevertAid™ First Strand cDNA Synthesis Kit
Single/Dual Luciferase® Reporter Assay System
TOPO TA Cloning® Kit (pCR®2.1-Topo Vector)
Viral RNA Isolation NucleoSpin Multi-96 Virus
Z-Competent E. coli Transformation Kit and Buffer SetTM
Amersham Biosciences, USA
Peqlab, Biotech, Erlangen
ID Vet, Frankreich
Peqlab, Erlangen
ID Vet, Frankreich
PBL, USA
Macherey-Nagel, Düren
Fermentas, St-Leon-Rot
Qiagen, Hilden
Stratagene, USA
Fermentas, St-Leon-Rot
Promega, Mannheim
Stratgene, USA
Macherey-Nagel, Düren
Zymo Research, USA
Tabelle 3.8: Verwendete Kit-Systeme
3.9 Radioaktivität
α[32P]dCTP
Amersham Biosciences, USA
3.10 Puffer und Nährmedien
3.10.1 Behandlung von Lösungen und Geräten
Es wurde nur mit sterilen Medien und Materialien gearbeitet. Hitzestabile Lösungen wurden
autoklaviert (121°C, 2 bar, 20 Minuten), hitzelabile Lösungen wurden steril filtriert
(Porendurchmesser 0,2 µm). Glasgeräte und Gerätschaften, die größere thermische
Belastungen überstehen, wurden durch trockene Heißluft sterilisiert (180°C, 1,5 Stunden).
3.10.2 Puffer
1×PBS:
140 mM NaCl
8,1 mM Na2HPO4
2,7 mM KCl
1,5 mM KH2PO4
pH 7,4
E
29
Material und Methoden
Bei den Experimenten wurde für Zellkulturen PBS ohne Ca2+ und Mg2+ verwendet und zum
Waschen und Fixieren von infizierten Zellen für Immunfärbungen PBS mit Ca2+ und Mg2+.
Avicelmedium (1ml):
0,5 ml DMEM 2×
0,5 ml Avicel 3%
5 µl BSA 10%
Kristallviolettlösung:
10 g Kristallviolett
200 ml Ethanol
800 µl ddH2O.
DNA-Gelelektrophorese:
50×TAE:
2 M Tris
1 M Essigsäure
0,1 M EDTA
pH 8,3
Ladepuffer (Elektrophoresegele) :
0,25% Bromphenolblau
0,25% Xylencyanol F
30% Glycerin
Western Blot:
4×Lämmli-Puffer:
400 mM Tris-HCl (pH 6,8)
8% SDS
40% Glycerin
65 mM DTT
12,5 µM Bromphenolblau
Trenngelpuffer:
1,5 M Tris/HCl, pH 8,8
0,4% SDS
E
30
10% Trenngel:
2,5 ml Trenngelpuffer
3,3 ml 30% Acrylamid mit 0,8% Biasacrylamid
4,1 ml ddH2O.
50 µl 10% APS
5 µl TEMED
Sammelgelpuffer:
0,5 M Tris/HCl, pH 6,8
0,4% SDS
5% Sammelgel:
1,25 ml Sammelgelpuffer
0,82 ml 30% Acrylamid mit 0,8% Bisacrylamid
2,80 ml ddH2O.
25 µl 10% APS
5 µl TEMED
10× Laufpuffer:
250 mM Tris/HCl, pH 8,3
14,4% Glycin
1% SDS
Transferpuffer:
25 mM Tris/HCl
186 mM Glycin
20% Methanol
Lysepuffer:
50 mM Hepes
125 mM NaCl
1% NP40
1 mM EDTA
0,5% Natriumdeoxycholat
0,1% SDS
100 U/ml Benzonase
1 mM DTT
2,5 µl/ml Protease-Inhibitor
Material und Methoden
E
31
Northern Blot:
10×MOPS:
200 mM MOPS
50 mM NaOAc
10 mM EDTA-Na
add 1l ddH2O
pH 7
20×Probenpuffer:
0,8% Bromphenolblau
0,8% Xylencyanol FF
50% Glycerol
add 4 ml ddH2O
20×SSC:
3 M NaCl
0,3 M Na-Citrat
add 1l ddH2O
pH 7
RNA-Ladepuffer:
5 µl ddH2O
10 µl Formamid
2 µl Formaldehyd (37%)
2 µl 10×MOPS
1 µl 20×Probenpuffer
0,1 µl Ethidiumbromid (10mg/ml)
denaturierendes RNA-Agarosegel (1,2%): 160 ml ddH2O
2,4 g Agarose
20 ml 10×MOPS
20 ml Formaldehyd (37%)
Laufpuffer:
1300 ml ddH2O
160 ml 10×MOPS
140 ml Formaldehyd (37%)
Material und Methoden
E
32
50×Denhardt’s:
1% Ficoll
1% Polyvinylpyrrolidon
1% BSA
add 500 ml ddH2O
Hybridisierungslösung:
5×Pipes
2×Denhardt’s
50% Formamid
0,2% SDS
200 µg/ml ssDNA
add 10 ml ddH2O
10× Pipes:
30,2 g Pipes in 600 ml ddH2O
100 mM NaOH (pH 6,8)
3 M NaCl
100 mM EDTA (pH 8)
add 1l ddH2O
Proteinaufreinigung:
Beschallungspuffer: 20 mM Na-Phosphat-Puffer pH 7,8
300 mM NaCl
10 mM β-Mercaptoethanol
Puffer A:
6 M Guanidiniumhydrochlorid
0,1 M NaH2PO4
0,01 M Tris-HCl
10 mM β-Mercaptoethanol
Puffer B:
8 M Harnstoff
0,1 M NaH2PO4
0,01 M Tris-HCl
10 mM β-Mercaptoethanol
Material und Methoden
E
33
Puffer B’:
Material und Methoden
2 M Harnstoff
1 M NaCl
0,1 M NaH2PO4
0,01 M Tris-HCl
10 mM β-Mercaptoethanol
Puffer E I:
0,05 M Na-Acetat
1 M NaCl
0,01 M Tris-HCl
2 M Harnstoff
10 mM β-Mercaptoethanol
Puffer E II:
0,05 M Na-Acetat
1 M NaCl
2 M Harnstoff
10 mM β-Mercaptoethanol
3.10.3 Nährmedien für Bakterien
XL1-Blue Z-kompetente E. coli-Bakterien und chemisch kompetente OneShot®TOP10-Zellen
und BL21 wurden in Luria-Bertani-Medium (LB) kultiviert.
LB-Medium:
10 g/l Bacto Trypton
5 g/l Hefeextrakt
5 g/l NaCl
add 1000 ml ddH2O
pH 7
autoklavieren
Antibiotika wurden in der Konzentration 100 µg/ml zugegeben. Für die Kultivierung von
Bakterien auf Agarplatten wurde 1,5% BactoTM Agar zugegeben.
Für die Transformation der Bakterien mit Hitzeschock wurde S.O.C.-Medium verwendet.
E
34
S.O.C.-Medium:
Material und Methoden
20,0 g Bacto™ Trypton
5,0 g Hefeextrakt
0,5 g NaCl
add 1000 ml ddH2O.
autoklavieren
Zugabe von 10 ml steril-filtriertes 1 M MgCl2 und 10 ml steril filtriertes
MgSO4.
Zugabe von 10 ml steril filtrierte 2 M Glucose.
Für die Herstellung kompetenter Bakterien wurde SOB-Medium verwendet.
SOB-Medium:
0,5% Hefeextrakt
2 mM Bacto™ Trypton
10 mM NaCl
2,5 mM KCl
.
10 mM MgCl2
10 mM MgSO4
pH 6,8-7
Das Medium wurde ohne Mg2+ hergestellt und 20 Minuten bei 121°C
autoklaviert. Vor Gebrauch wurde dem Nährmedium 20 mM einer
2M Mg2+-Lösung zugegeben.
3.10.4 Zellkulturmedien
293T-, MDCKII-, MDCK-NS1-GFP- und L929-Zellen wurden in Dulbecco’s modified Eagle
medium (DMEM) mit 10% fötalem Kälberserum (FKS) kultiviert. CEC-32 und CEF wurden
in DMEM mit 8% FKS und 2% Hühner-Serum kultiviert. Das Medium enthielt zusätzlich
526,6 mg/l Glutamin, sowie 1 mM NaOH. Als vorbeugende Maßnahme gegen bakterielle
Kontaminationen wurde dem Kulturmedium 50.000 E/l Penicillin und 50 mg/l Streptomycin
zugesetzt. Für die Zellkulturen wurden des Weiteren PBS ohne Ca2+ und Mg2+ zum Waschen
sowie Trypsin/EDTA-Lösung (0,05% Trypsin 1:1250; 0,16% EDTA Dinatriumsalzdihydrat)
zum Ablösen der Zellen verwendet. Die Zellen wurden in einem Luftbefeuchtungsinkubator
bei 37°C unter 5% CO2 gehalten.
Zur Infektion von Zellen mit Virus wurde für die Dauer der Infektion DMEM mit 2% FKS
und 10 mM Hepes verwendet.
E
35
DMEM komplett
Material und Methoden
100 ml DMEM
37 ml 10% NaHCO3 (w/v)
10 ml 100 mM Sodiumpyruvat
16 ml 250 mM Glutamin
2,4 ml 1 M NaOH
add 1000 ml ddH2O
3.10.6 Anästhesie der Versuchstiere
Ketamin-Rompun-Anästhesie (5ml):
500 µl 10% Ketavet® Essex Tierarznei, München
125 µl 2% Rompun® Bayer AG, Leverkusen
437 µl 0,9% NaCl-Lösung
3.11 Bakterien
Stamm
Genotyp
XL1-Blue (Stratagene)
recA1 endA1 gyrA96 thi-1 hsdR17 supE44 relA1 lac
[F’ proAB lacIqZ.M15 Tn10 (Tetr)]
[F- mrcA ∆(mrr-hsdRMS-mcrBC) Φ80lacZ ∆(araleu)7697 galU galK rpsL (StrR) endA1 nupG]
F- mrcA ∆mrr-hsdRMS-mrcBC) Φ80dlacZ ∆M15
∆lac74 deoR recA1 endA1 araD139 ∆(ara, leu)7697
galU galK λ- rpsL nupG
F-, dcm, ompT, hsdS(rB-mB-), gall(DE3) [pLysS amr]
OneShot®TOP10 (Invitrogen)
DH10BTM (Gibco BRL®)
BL21 (Stratagene)
Tabelle 3.9: Verwendete Bakterien-Stämme
3.12 Viren
Virus
Referenz
SC35-wt (A/seal/Mass/1/1980) (H7N7)
SC35-delNS1
SC35-NS1(73)
SC35-NS1(99)
SC35-NS1(126)
R65-wt (A/Cygnus cygnus/Germany/R65/2006) (H5N1)
R65-delNS1
R65-NS1(SC35)
R65-trunkNS1
J. Stech
diese Arbeit
diese Arbeit
diese Arbeit
diese Arbeit
diese Arbeit
diese Arbeit
diese Arbeit
diese Arbeit
Tabelle 3.10: Verwendete Viren
E
36
Material und Methoden
3.13 Interferone
Interferon
Referenz
Rekombinantes humanes Hybrid-Interferon αB/D
Hühner-Interferon-α
Gangemi et al., 1989
Schultz et al., 1995
Tabelle 3.11: Verwendete Inteferone
3.14 Zellen
Zelllinie
Herkunft/Morphologie
Spezies
293T
A549
MDCK II
MDCK-NS1-GFP
CEC-32
CEF
epitheliale embryonale Nierenzellen
Lungenkarzinomepithelzellen
epitheliale Nierenzellen
epitheliale Nierenzellen
permamente Fibroblasten
primäre Fibroblasten
Homo sapiens (Mensch)
Homo sapiens (Mensch)
Canis familiaris (Hund)
Canis familiaris (Hund)
Coturnix coturnix (Wachtel)
Gallus gallus (Huhn)
Tabelle 3.12: Verwendete Zelllinien
3.15 Mausstämme
Stamm
Herkunft
B6.A2G-Mx1 (B6-Mx1)
durch Rückkreuzung des Mx1-Allels aus Stamm A2G erhalten
(Stäheli et al., 1985)
durch Rückkreuzung des Mx1-Allels erhalten
Lienenklaus et al., 2009
BALB-Mx1
IFN-β-LUC-Mäuse
Tabelle 3.13: Verwendete Mausstämme
3.16 Antikörper
Fluorochrom-konjugierte Sekundärantikörper wurden von Dianova (Hamburg) verwendet.
Antikörper
Herkunft
Spezifität
Epitop
Verdünnung
Maus-anti FluA NP (AbD,
Serotec, Gemany)
Kaninchen-anti NS1 (1-73)
Maus-anti-β-Tubulin
Kaninchen-anti-Aktin
Maus
monoklonal
FluA NP
1:1000
Kaninchen
Maus
Kaninchen
polyklonal
monoklonal
polyklonal
FluA NS1
β-Tubulin
Aktin
1:4000
1:1000
1:1000
Tabelle 3.14: Verwendete Primärantikörper
E
37
Material und Methoden
Antikörper
Herkunft
Spezifität
Epitop
Verdünnung
Anti-Maus-IgG/HRP (Dako)
Anti-Maus-HRP (Amersham)
Anti-Kaninchen-HRP
(Amersham)
Kaninchen
Schaf
Maus
polyklonal
polyklonal
polyklonal
Maus-IgG
Maus-IgG
Kaninchen-IgG
1:2000
1:10000
1:10000
Tabelle 3.15: Verwendete Sekundärantikörper
3.17 Oligonukleotide
Name
Sequenz (5’ – 3’)
SC35_PB2_597-614
SC35_PB1_561-580
SC35_PA_284-203
SC35_HA_574-595
SC35_NP_679-698
SC35_NA_549-567
SC35_M_402-421
SC35_PB2_1101-1122
SC35_PB1_1352-1371
SC35_PA_962-983
SC35_NP_461-482
SC35_PA_1032-1052
SC35_NS_1-73
SC35_NS_889-875
SC35_NP_566_for
SC35_NP_67_92_for
SC35_NP_1498_1473_rev
SC35_NP_566_541_rev
SC35_NP_566_541_rev
SC35_NS_UTR-for
SC35_NS_UTR_rev
SC35delNS1_HA_UTR_1-24
SC35delNS1_HA_UTR_1740-1717
SC35_NS_Seq_UTR_for
SC35_NS_Seq_UTR_rev
GGAGAAACTCCAGGATTG
GGAAATAACAACGCACTTCC
CCTGGACAGTGGTAAATAGC
GCTCTGATAGTTTGGGGAATTC
GGGCGGAGAACAAGAATTGC
GATGGTCCAGCACTAGTTG
GTTGCATGGGCCTCATATAC
GGGGTATGAAGAGTTCACAATG
CCTCTGATGACTTTGCTCTC
CCTTTTTCGGCTGGAAAGAGCC
GGCATTCCAACCTGAATGATGC
GGCTTGGAAGCAAGTGCTAGC
CAAAAGCAGGGTGAC
CACCCTTGTTTCTAC
CTGATGCAAGGTTCAACTCTTCCAAG
CGATCTTATGAGCAGATGGAAACTGG
GCCTTCCTTTGACATGAATAACGAGG
CTTGGAAGAGTTGAACCTTGCATCAG
CTTGGAAGAGTTGAACCTTGCATCAG
GCAAAAGCAGGGTGACAAAAAC
GTAGAAACAAGGGTGTTTTTTATC
AGCAAAAGCAGGGGATACAAAATG
AGTAGAAACAAGGGTGTTTTTCTC
GCAAAAGCAGGGTGACAAAAAC
GTAGAAACAAGGGTGTTTTTTATC
Tabelle 3.17: Verwendete Oligonukleotide für Sequenzierung (SC35)
E
38
Material und Methoden
Name
Sequenz (5’ – 3’)
R65_PB1_for_511_534
R65_PB1_for_1001_1024
R65_PB1_for_1500_152
R65_PB1_for_2000_2021
R65_PB2_for_502_523
R65_PB2_for_1003_1025
R65_PB2_for_1501_1524
R65_PB2_for_2001_2024
R65_PA_for_500_520
R65_PA_for_1000_1020
R65_PA_for_1501_1524
R65_HA_for_501_524
R65_HA_for_1003_1027
R65_M_for_500_522
R65_NA_for_501_524
R65_NP_for_500_523
NS_R65_UTR_for
NS_R65_UTR_rev
R65_NS1_50_29_Seq_pHW2000
R65NS1_819_841_Seq_pHW2000
pHW2000_499_520
pHW2000_1000_4154
pHW2000_1500_1520
pHW(reverse)(167-785
pHW(sense)(2912-2932)
CTAATAGATTTCCTCAAGGATGTG
CAAGGAACCAGCCAGAATGGTTTT
CACGAGCTTTTTCTACCGCTATGG
CCGTTGCAACTACGCATTCATG
GCACAAGATGTCATCATGGAGG
GGAGGCCTCACTTTCAAAAGAAC
GAGAGAGTAGTTGTAAGCATTGAC
CAATAAGGCAACCAAAAGACTTAC
CGGACTACACCCTTGATGAAG
CATGAAAAGGGTATAAACCCC
GAAGGAAGACGGAAAACTAATCTG
CCTTTTTTAGAAATGTGGTATGGC
CAGATTAGTCCTTGCGACTGGGCTC
CATCGGTCTCACAGACAGATGGC
GCAAGTGCTTGCCATGATGGCACC
GAGCTCTCGTACGTACTGGAATGG
AGCAAAAGCAGGGTGACAAAAAC
AGTGAAACAAGGGTGTTTTTTAT
GCTTGACACAGTGTTGGAATGC
GATAAGAACCTTCTCGTTTCAGC
GGATTGGGAAGACAATAGCAGG
CAATGCTCACGCTGTAGGTATC
CCTTTTAAATTAAAAATGAAG
GGGGACAGGTGTCCGTGTC
GAGAACCCACTGCTTACTGGC
Tabelle 3.19: Verwendete Oligonukleotide für Sequenzierung (R65)
Name
Sequenz (5’ – 3’)
chIFNα_for
chIFNα_rev
ch_actin_β_for
ch_actin_β_rev
chIFNβ_for
chIFNβ_rev
chMx_60_80_for
chMx_590_570_rev
R65_NP_for_51_76
R65_NP_rev_498_472
R65_NS1_for_40_62
R65_NS1_rev_752_730
SC35_NP_67_92_for
SC35_NP_566_541_rev
SC35_NS_41_64_for
SC35_NS_566_541_rev
CAACGCGAGTCCCACCATGGCTG
GGTGCGTTTGGGGCTAAGTGCGC
CTGTATGCCTCTGGTCGTACCAC
GTTTCATGGATACCACAGGACTCC
GACTGCAAACCATCAGTCTCCAG
CACTGGGTGTTGAGACGTTTGG
GCAGAATAGTAATGTACCACC
GTGCCAGCCACTATATCTTGG
GTCTCAAGGCACCAAACGATCTTATG
CGTTCTCTGATATGTGGCATCATTTCG
CTGTGTCAAGCTTTCAGGTAGAC
GTAATTTTCAATCTATGTCGTATTTC
CGATCTTATGAGCAGATGGAAACTGG
CTTGGAAGAGTTGAACCTTGCATCAG
TGTATCAAGCTTTCAGGTAGA
TGTCGCACTTCTTCAATCAGC
Tabelle 3.18: Verwendete Oligonukleotide für RT-PCR
E
39
Material und Methoden
3.18 Plasmide
Plasmid
Beschreibung
Referenz
pHW2000_SC35_PB2
AmpR, PB2-Gen von SC35, pol I- und
hCMV-Promotor (bidirektional)
AmpR, PB1-Gen von SC35, pol I- und
hCMV-Promoter (bidirektional)
AmpR, PA-Gen von SC35, pol I- und hCMVPromoter (bidirektional)
AmpR, HA-Gen von SC35, pol I- und
hCMV-Promoter (bidirektional)
AmpR, NP-Gen von SC35, pol I- und hCMVPromoter (bidirektional)
AmpR, NA-Gen von SC35, pol I- und
hCMV-Promoter (bidirektional)
AmpR, M-Gen von SC35, pol I- und hCMVPromoter (bidirektional)
AmpR, NS-Gen von SC35, pol I- und hCMVPromoter (bidirektional)
AmpR, PB2-Gen von R65, pol I- und hCMVPromoter (bidirektional)
AmpR, PB1-Gen von R65, pol I- und hCMVPromoter (bidirektional)
AmpR, PA-Gen von R65, pol I- und hCMVPromoter (bidirektional)
AmpR, HA-Gen von R65, pol I- und hCMVPromoter (bidirektional)
AmpR, NP-Gen von R65, pol I- und hCMVPromoter (bidirektional)
AmpR, NA-Gen von R65, pol I- und hCMVPromoter (bidirektional)
AmpR, M-Gen von R65, pol I- und hCMVPromoter (bidirektional)
AmpR, NS-Gen von R65, pol I- und hCMVPromoter (bidirektional)
AmpR, NS-Gen von R65 (inklusive NS1 und
UTR), CMV-Promoter
AmpR, NS1(1-126)-Gen (inklusive NS1 und
UTR) von R65, CMV-Promoter
AmpR, NS(delNS1)-Gen (inklusive NS1 und
UTR) von R65, CMV-Promoter
AmpR, Renilla-Luc, SV40-Promoter
AmpR, enthält FF-Luc unter Kontrolle des
Mx1-Promoters
AmpR, enthält FF-Luc unter Kontrolle des
chicken Mx-Promoters
AmpR, prokaryotischer Expressionsvektor
J.Stech
pHW2000_SC35_PB1
pHW2000_SC35_PA
pHW2000_SC35_HA
pHW2000_SC35_NP
pHW2000_SC35_NA
pHW2000_SC35_M
pHW2000_SC35_NS
pHW2000_R65_PB2
pHW2000_R65_PB1
pHW2000_R65_PA
pHW2000_R65_HA
pHW2000_R65_NP
pHW2000_R65_NA
pHW2000_R65_M
pHW2000_R65_NS
pCAGGs_R65_NS
pCAGGS_R65_NS1(1-126)
pCAGGS_R65_NS(delNS1)
pRL_SV40
pGL_3_Mx1 P
pHSIIa_chMxP
pET-3a/chIFN-β
Tabelle 3.16: Verwendete Plasmide
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
J.Stech
diese Arbeit
diese Arbeit
Promega
Georg Kochs
B. Schumacher
C. Rinderle
E
40
Material und Methoden
3.19 Zellkulturarbeiten und virologische Methoden
3.19.1 Zellkultivierung
Die aviären Zelllinien wurden in DMEM mit 8% FKS und 2% Hühnerserum gehalten, alle
anderen Zelllinien wurden in DMEM mit 10% FKS gehalten. Bei Konfluenz des Zellrasens
wurden die Zellen geteilt. Nach dem Waschen mit vorgewärmtem PBS wurden die Zellen mit
Trypsin/EDTA-Lösung behandelt, um sie vom Boden der Zellkulturflasche abzulösen. Neun
Zehntel der Zellsuspension wurden verworfen und anschließend wurde mit DMEM aufgefüllt.
3.19.2 Herstellung von Trachealorgankulturen aus Hühnerembryonen
Für die gesamte Herstellung war es wichtig, dass das verwendete Medium stets 37°C hatte,
und dass die Herstellung möglichst zügig vonstatten ging.
18-19 Tage alte befruchtete SPF-Hühnereier (Lohmann, Cuxhafen) wurden geöffnet und
möglichst schnell mit der Schere dekapitiert und der Dottersack wurde abgetrennt. Der
Embryo wurde in eine sterile Petrischale gelegt und seziert. Die Trachea wurde freigelegt und
in der Brusthöhle hinter der Bifurkation abgetrennt. Die Trachea wurde sofort in ein mit
Medium 199 Hanks’ gefülltes 50 ml-Falcon gegeben und gevortext. Anschließend wurde ein
steriles Filterpapier mit vorgewärmtem Medium getränkt. Die Trachea wurde auf das
Filterpapier unter eine Lupenlampe gelegt. Mit dem Skalpell und Pinzetten wurde die Trachea
vom Bindegewebe befreit. Anschließend wurde die Trachea mit Hilfe einer Mikrotomklinge
und einer gebogenen Pinzette in dünne Ringe geschnitten (ca. 0,5-0,8 mm). Diese
Trachealringe wurden schnell in eine mit vorgewärmtem Medium gefüllte Petrischale
überführt. Danach wurden die Ringe einzeln in 5ml-Transfektionsröhrchen mit Deckel, die
600 µl Medium enthielten, überführt und sofort im Überkopfschüttler bei 37°C ohne CO2
inkubiert. Nach 48 Stunden wurden die Trachealringe auf Überleben selektiert. Es wurden nur
Ringe mit 100%iger Ziliaraktivität ausgesucht, der Rest wurde verworfen.
3.19.3 Transfektion
Zur
Transfektion
von
DNA
in
Säugerzellen
wurde
das
Liposomen-Reagenz
Lipofectamine™ 2000 verwendet. Die Zellen wurden in Loch-Platten ausgesät, so dass sie am
Tag der Transfektion eine 70%ige Konfluenz aufwiesen. Es wurden 0,5-8,0 µg DNA in 50 µl
OptiMEM® gegeben. Parallel dazu wurden 2 µl Lipofectamine™ 2000 je µg DNA in 250 µl
OptiMEM®
gegeben.
Anschließend
wurde
die
DNA-Lösung
vorsichtig
in
die
E
41
Material und Methoden
Transfektionslösung getropft und für 20 Minuten bei Raumtemperatur inkubiert. Nach der
Inkubationszeit wurde die DNA/Transfektionslösung auf die Zellen getropft. Nach ca.
20 Stunden wurde ein Mediumwechsel vorgenommen.
Für die Transfektion von CEC-32 wurde das Transfektionsreagenz Nanofectin verwendet. Es
wurden 3,2 µl Nanofectin je µg DNA verwendet und in 50 µl Verdünnungspuffer getropft.
Die DNA wurde ebenfalls in 50 µl Verdünungspuffer gegeben. Nach 5-minütiger Inkubation
bei Raumtemperatur wurde die DNA-Lösung vorsichtig zu der Nanofectin-Lösung getropft
und nach weiteren 20 Minuten Inkubation wurde die gesamte Lösung vorsichtig auf die
Zellen getropft. Nach ca. 20 Stunden wurde ein Mediumwechsel vorgenommen.
3.19.4 Dualer Luziferase-Reportertest
Die Stimulation des Firefly-Luziferase-Reporters durch IFN wurde mit Hilfe eines Dualen
Luziferase Reportertests gemessen. CEC-32 wurden in 12-Loch-Platten ausgesät und wie
unter 3.19.3 beschrieben mit 0,1 des Reporterkonstruktes pHSIIa_chMxP transfiziert. Um
Unterschiede in der Transfektionseffizienz und im Zelltod während des Versuchs
auszugleichen, wurde zusätzlich 0,1 µg des durch den konstitutiven SV40-Promoter
kontrollierten Renilla-Luziferase-Reporterplamids pRL-SV40 transfiziert. Zusätzlich wurden
Expressionskonstrukte für verschiedene Varianten von NS1 kotransfiziert. Nach 12-stündiger
Inkubation bei 37°C wurde das Medium abgesaugt und IFN-haltiges Medium (1000 U/ml)
dazugegeben. Nach weiteren 12 Stunden Inkubation wurde das Medium abgesaugt und die
Zellen wurden mit 1×Passive Lysis Buffer für 10 Minuten bei Raumtemperatur lysiert. 10 µl
Lysat wurden in einem 4 ml Luminometerröhrchen vorgelegt und nach Zugabe von 5 µl
Firefly-Luziferase-Assay-Reagenz wurde die der Firefly-Luziferase-Aktivität entsprechende
Chemilumineszenz gemessen. Mit 50 µl Stop&Glo-Substrat wurde die Aktivität der FireflyLuziferase inhibiert und die Aktivität der Renilla-Luziferase gemessen.
3.19.5 Infektion mit Influenza-A-Viren für Wachstumskurven
MDCK-NS1-GFP beziehungsweise CEF wurden 24 Stunden vor Infektion so in 6-LochPlatten eingesät, dass sie am folgenden Tag eine 70%ige Konfluenz aufwiesen. Die Zellen
wurden dann 1x mit PBS gewaschen und mit einer multiplicity of infection (MOI) von 0,001
für eine Stunde in PBS/0,3%BSA bei Raumtemperatur infiziert. Dann wurde das Inokulum
abgenommen und die Zellen wurden 3x mit PBS gewaschen. Zur weiteren Kultivierung
wurde Infektionsmedium verwendet (DMEM mit 2% FKS, 10mM Hepes, Penicillin,
E
42
Material und Methoden
Streptomycin). Nach 0, 12, 24, 36, 48 und 60 Stunden wurden 50 µl entnommen und der
Virustiter wurde mittels Immunfärbung bestimmt (Kapitel 3.19.7).
Bei der Erstellung von Wachstumskurven auf Trachealorgankulturen wurden die Ringe 1x mit
PBS gewaschen und dann mit der jeweiligen Virusmenge für eine Stunde bei 37°C infiziert in
100 µl Medium 199 Hanks’. Anschließend wurde das Inokulum abgenommen und die Ringe
3x
mit
PBS
gewaschen.
Zur
weiteren
Kultivierung
wurden
wiederum
600 µl
Medium 199 Hanks’ verwendet und die Ringe im Überkopfschüttler bei 37°C inkubiert. Alle
12 Stunden wurden 50 µl entnommen und der Virustiter wurde mittels Immunfärbung
bestimmt.
Für die Wachstumskurven nach IFN-Behandlung wurden die Zellen beziehungsweise die
Trachealringe für 8 beziehungsweise 24 Stunden mit IFN-haltigem Medium inkubiert. Nach
der entsprechenden Zeit wurden die Zellen wie oben beschrieben infiziert und anschließend
wurde wiederum IFN-haltiges Medium dazugegeben und alle 12 Stunden wurden 50 µl
Überstand entnommen.
3.19.6 Herstellung rekombinanter Influenza-A-Viren
Im Rahmen dieser Arbeit wurden rekombinante Influenza-A-Viren hergestellt. Es wurden
acht bidirektionale Expressionsvektoren eingesetzt. Eine Kokultur von 293T- und MDCKNS1-GFP-Zellen wurde mit den Vektoren transfiziert. Von jedem Plasmid wurden 0,5 µg
eingesetzt, so dass sich bei 8 Plasmiden pro Ansatz eine DNA-Menge von 4 µg ergab. Die
Transfektion wurde wie in 3.19.3 beschrieben unter Verwendung des Transfektionsreagenz
Lipofectamine™ 2000 durchgeführt.
Die
293T-
und
MDCK-NS1-GFP-Zellen
wurden
zunächst
in
insgesamt
12 ml
Zellkulturmedium aufgenommen und dann 5 Minuten bei 900 rpm (revolutions per minute)
abzentrifugiert. Das so gewonnene Zellpellet wurde daraufhin in 3,5 ml DMEM mit 2% FKS
und 10 mM Hepes (Glutamin, Penicillin und Streptomycin) resuspendiert.
Nach
abgelaufener
Inkubationszeit
wurden
250 µl
der
Zellsuspension
zu
jedem
Transfektionsansatz in das Polystyrolröhrchen gegeben, kurz durchmischt und dann in ein
Loch einer 6-Loch-Schale gegeben.
Der Ansatz wurde für 20 Stunden bei 37°C inkubiert. Danach wurde das Medium
abgenommen und 1,5ml DMEM mit 2% FKS, 10 mM Hepes, Penicillin und Streptomycin
zugeführt.
Bei einsetzendem CPE (cytopathischen Effekt) konnte das Medium, das nun rekombinante
Viren enthielt, abgenommen und kurz abzentrifugiert werden.
E
43
Material und Methoden
Um Virusstocks zu erhalten, wurde der gesamte Überstand für eine Stunde auf neue MDCKNS1-GFP-Zellen gegeben. Nach 1 Stunde Inkubation bei Raumtemperatur wurde der
Überstand abgenommen und Medium mit 2% FKS, 10mM Hepes, Penicillin und
Streptomycin zugeführt. Wiederum wurde auf einen einsetzenden CPE gewartet.
Anschließend wurde der Überstand abgenommen und zentrifugiert. Der Titer des so
gewonnen Virusstocks wurde wie in 3.19.7 beschrieben bestimmt.
3.19.7 Immunfärbung für die Virustiterbestimmung
MDCKII beziehungsweise MDCK-NS1-GFP-Zellen wurden 24 Stunden vor der Infektion im
Verhältnis 1:4 in eine 96-Loch-Platte ausgesät. Mit der zu untersuchenden Probe wurde eine
logarithmische Verdünnungsreihe in PBS mit 0,3% BSA durchgeführt. Anschließend wurden
die Zellen 1x mit PBS gewaschen und mit 50 µl/Loch der jeweiligen Virusverdünnungen
infiziert. Nach 1 Stunde wurde die Verdünnung abgesaugt und der Zellrasen mit 100 µl
Avicelmedium/Loch überschichtet und bei 37°C inkubiert.
24 Stunden nach der Infektion wurden die Zellen für 30 Minuten bei 4°C mit 3%
Paraformaldehyd in PBS fixiert, 3x mit PBS gewaschen und danach für weitere 15 Minuten
mit 0,5% Triton X-100 in PBS mit 20 mM Glycin in PBS permeabilisiert. Anschließend
wurden die fixierten Zellen wiederum 3x mit 0,05% Tween-80 in PBS gewaschen.
Als Primärantikörper wurde ein monoklonaler anti-Nukleoprotein-Antikörper aus dem
Kaninchen in einer Verdünnung von 1:1000 verwendet. Die Verdünnung wurde in 0,05%
Tween-80 in PBS mit 10% FKS eingesetzt. Als Sekundärantikörper wurde ein HRP
(horseradish peroxidase)-gekoppelter, polyklonaler Kaninchen anti-Maus ImmunglobulinAntikörper verwendet. Der Antikörper wurde in einer Verdünnung von 1:2000 ebenfalls in
0,05% Tween-80 in PBS mit 10% FKS angesetzt. Beide Inkubationsschritte wurden bei
Raumtemperatur durchgeführt. Nach erneutem 3maligem Waschen mit 0,05% Tween-80 in
PBS wurden 50 µl TrueBlue™ als HRP-Substrat für 30 Minuten auf die Zellen gegeben. Als
letztes wurde die 96-Platte mit ddH2O. gewaschen und getrocknet. Durch Auszählen der
gefärbten Zellen konnte der Virustiter der Probe in focus forming units (ffu) pro Milliliter
bestimmt werden.
3.19.8 Virusinaktivierung
Für die Bestimmung des IFN-Gehalts mittels ELISA (enzyme-linked immunosorbent assay)
(siehe 3.23.4) musste das in den Proben enthaltene Virus inaktiviert werden, um die Proben
E
44
Material und Methoden
unter BSL2-Bedingungen verwenden zu können. Das β-Propiolactone wurde in einer
Konzentration von 0,05% verwendet. Dazu wurde es zuerst 1:100 mit ddH2O verdünnt und
gevortext. Anschließend wurde die entsprechende Menge zu den jeweiligen Proben gegeben
und bei 4°C für 16 Stunden inkubiert. Um das β-Propiolactone für den ELISA zu
hydrolysieren, wurden die Proben für 2 Stunden bei 37°C inkubiert.
3.19.9 Bioassay zur Detektierung von induziertem Hühner-Interferon
Die Reporterzelllinie CEC-32 exprimiert stabil das Luziferasegen als Reportergen unter
Kontrolle des aviären Typ I IFN-induzierbaren Mx-Promotors. Die Behandlung der
Indikatorzellen mit Typ I IFN führt über die Bindung an den Typ I IFN-Rezeptor zur
Auslösung der JAK/STAT-Signalkaskade und somit zur Aktivierung des Mx-Promotors.
Dadurch wird die Luziferase-Expression induziert. Die Luziferase-Aktivität kann dann im
Luminometer gemessen werden (203).
Die Indikatorzellen wurden für 6 Stunden mit Überständen von infizierten Zellen behandelt.
Zusätzlich wurde ein Hühner-IFN-Standard mit bekannter Unit-Menge verwendet. Nach
6 Stunden Inkubation wurden die Zellen lysiert und die Luziferase-Aktivität im Luminometer
gemessen. Die absoluten Werte wurden mit dem Standard verrechnet und in Units/ml
angegeben.
3.20 DNA-Standardtechniken
3.20.1 Minipräparation von Plasmid-DNA
Diese Methode wurde angewendet, um kleine Mengen (~20 µg) an Plasmid-DNA aus
transformierten Bakterien für Restriktionsanalysen oder zur Sequenzierung zu gewinnen. Eine
Einzelkolonie wurde in 5 ml LB-Medium, das 100 µl/ml des geeigneten Antibiotikums
enthielt bei 37°C und 200 rpm auf einem Horizontalschüttler über Nacht inkubiert. Die
Minipräparation wurde nach Anleitung des Herstellers (Peqlab, E.Z.N.A. Miniprep Kit)
durchgeführt.
Die Elution der Plasmid-DNA erfolgte mit 30-50 µl Elutionspuffer oder sterilem Wasser. Die
DNA-Konzentration wurde in einem Spektralphotometer quantifiziert und die DNA bei 4°C
gelagert.
E
45
Material und Methoden
3.20.2 Midipräparation von Plasmid-DNA
Midipräparationen von Plasmid-DNA erfolgten mit Hilfe kommerziell erhältlicher Kits nach
Anleitung des Herstellers (Macherey-Nagel).
Dazu wurde, wie in 3.20.1 beschrieben eine Vorkultur angelegt. Von dieser wurde ein Aliquot
in einen Erlenmeyerkolben mit 50 ml LB-Medium (versetzt mit 100 µl/ml des jeweiligen
Antibiotikums) überführt und für 12-16 Stunden in einem Horizontalschüttler bei 200 rpm
und 37°C inkubiert. Nach erfolgter Plasmidaufreinigung wurde das Pellet in 100 µl TE-Puffer
oder
sterilem
Wasser
aufgenommen
und
die
DNA-Konzentration
in
einem
Spektralphotometer quantifiziert und die DNA bei 4°C gelagert
3.20.3 Restriktionsverdau
Um die DNA entweder für diagnostische oder für präparative Zwecke zu verdauen, wurden
Restriktionsendonukleasen nach Anleitung des Herstellers (Fermentas) verwendet. Es wurde
1 Unit (U) des Enzyms pro µg DNA in dem geeigneten Puffer für mindestens 1 Stunde bei
der jeweiligen Temperatur inkubiert. Anschließend wurde der Ansatz auf ein Agarosegel
aufgetragen (siehe 3.20.4).
3.20.4 Agarose-Gelelektrophorese
Zur gelelektrophoretischen Auftrennung von DNA wurden 1%ige oder 2%ige Agarosegele
mit 0,5 µg/ml Ethidiumbromid in 1×TAE-Puffer verwendet. Die Proben wurden mit
entsprechenden Volumina eines sechsfach konzentrierten Probenpuffers versetzt und
elektrophoretisch aufgetrennt. Die Auswertung erfolgte mittels UV-Licht.
3.20.5 Gelextraktion
Um die DNA nach einem Restriktionsverdau oder einer PCR-Reaktion zu reinigen, wurde
eine Gelextraktion durchgeführt. Hierbei wurde die gewünschte Bande aus dem Gel mit Hilfe
eines Skalpells ausgeschnitten, und anschließend wurde die DNA nach Anleitung des
Herstellers (Peqlab, E.Z.N.A Gel Extraction Kit) aus dem Gel eluiert. Dazu wurde das
ausgeschnittene Gelstück gewogen und in 100 µl Bindepuffer/100 µg gegeben, wobei davon
ausgegangen wurde, dass das Gel eine Dichte von ca. 1 g/ml hat. Diese Mischung wurde dann
bei 55°C für 7 Minuten inkubiert, bis sich das Gelstück vollständig aufgelöst hat, die DNA
wurde gereinigt und zuletzt in 30 µl Elutionspuffer eluiert.
E
46
Material und Methoden
Für den Fall, dass die PCR-Fragmente für weitere Klonierungen verwendet wurden, wurde
die Template-DNA durch Hinzufügen von 1 µl des Restriktionsenzyms DpnI (10 U) bei 37°C
verdaut.
3.20.6 PCR (polymerase chain reaction)
PCR wurde angewendet um spezifische DNA-Moleküle für Klonierungsreaktionen zu
amplifizieren. Hierzu wurde die Herculase II Fusion Enzyme-Polymerase von Invitrogen
verwendet, die proofreading-Aktivität besitzt. Als Matrize wurden 10-100 ng eingesetzt. Die
Standardreaktion wurde wie folgt durchgeführt, wobei auf 50 µl mit ddH2O aufgefüllt wurde:
5×Reaktionsmix
10 µl
Vorwärtsprimer (10 µM)
1,25 µl
Rückwärtsprimer (10 µM)
1,25 µl
Herculase II Fusion Enzyme
1 µl
DNA (10 – 100 ng)
x µl
ddH2O
x µl
Die PCR wurde unter folgenden Bedingungen durchgeführt:
initiale Denaturierung
10 min
95°C
-------------------------------------------------
Denaturierung
1 min
95°C
Hybridisierung
1 min
58°C
Elongation
1 min/kb
72°C
35 Zyklen
-------------------------------------------------
finale Elongation
10 min
72°C
3.20.7 TOPO® TA Cloning von PCR-Produkten
Um PCR-Produkte in pcDNA3.1/V5-His© TOPO® klonieren zu können, wurden 3’AÜberhänge durch Inkubation der extrahierten DNA mit Taq-Polymerase-Puffer (10×), dNTPs
(Gibco) (50 mM) und Taq Polymerase (5 U) für 10-15 Minuten bei 72°C generiert. Die
Klonierungsreaktion wurde wie folgt angesetzt:
E
47
Material und Methoden
1 µl PCR-Produkt
3 µl ddH2O
1 µl Salzlösung
1 µl TOPO®-Vektor
Die Proben wurden für 15 Minuten bei Raumtemperatur inkubiert und anschließend auf Eis
gestellt.
Von
dem
Klonierungsansatz
wurden
3 µl
für
die
Transformation
von
OneShot®TOP10 chemisch kompetenten E. coli verwendet. Hierfür wurden die Bakterien mit
der DNA für 15 Minuten auf Eis inkubiert und anschließend wurde ein Hitzeschock bei 42°C
für 2 Minuten durchgeführt. Nach Zugabe von 100 µl S.O.C.-Medium wurden die Zellen
1 Stunde bei 37°C inkubiert und anschließend auf vorgewärmten LB-Agarplatten, die über
Nacht bei 37°C inkubiert wurden ausgestrichen.
Zur Identifizierung von positiven Klonen wurde ein Restriktionsverdau (3.20.3) der MiniprepDNA (3.20.1) mit anschließender Gelelektrophorese (3.20.4) durchgeführt.
3.20.8 Dephosphorylierung linearisierter Plasmid-DNA
Der Rezirkularisierung linearisierter Plasmid-DNA kann durch Entfernung der terminalen 5’Phosphatgruppe entgegen gewirkt werden. Dazu wurde die DNA mit Shrimp alkaline
Phosphatase in einem Gesamtvolumen von 10 µl nach Anleitung des Herstellers (Roche)
behandelt.
8 µl
verdauter
DNA
wurden
mit
1 µl
SAP
(1 U)
und
1 µl
10×Dephosphorylierungspuffer für 10 Minuten bei 37°C inkubiert. Die Inaktivierung wurde
für 15 Minuten bei 65°C durchgeführt.
Die so dephosphorylierten Vektoren wurden für die im Folgenden beschriebene Ligation
verwendet.
3.20.9 Ligation von DNA-Fragmenten
Alle Ligationen wurden mit einem Vektor-Insert-Verhältnis von 1:3 unter Verwendung des
Rapid Ligation Kit (Fermentas MBI) durchgeführt. Bei einem Gesamtvolumen von 20 µl
wurden 4 µl 5×Rapid Ligation Buffer und 1 µl T4 DNA-Ligase (5 U) verwendet. Der Ansatz
wurde 5 Minuten bei Raumtemperatur inkubiert und anschließend wurden 2,5 µl für die
Transformation verwendet. Bei jeder Ligation wurden eine background-Kontrolle
(dephosphorylierter Vektor ohne Insert), eine Ligationskontrolle (linearisierter Vektor ohne
Insert) und eine Transformationskontrolle (nicht linearisierter Vektor) durchgeführt.
E
48
Material und Methoden
3.20.10 DNA-Sequenzierung
Alle Sequenzierungsreaktionen von DNA-Plasmiden wurden von GATC Biotech AG
(Konstanz) durchgeführt.
3.20.11 Ortsspezifische Mutagenese
Um Punktmutationen, Aminosäureaustausche, Deletionen oder Insertionen von Nukleotiden
zu entfernen, wurde eine ortsspezifische Mutagenese durchgeführt. Dazu wurden
Oligonukleotide verwendet, die die gewünschte Änderung in der Basenfolge aufwiesen. Beide
Primer enthielten den gewünschten Nukleotidaustausch und mussten an die gleiche Sequenz
am jeweils komplementären Strang binden. Die Reaktion wurde wie folgt angesetzt und mit
ddH2O auf 50 µl aufgefüllt.
10×Reaktionsmix
5 µl
Vorwärtsprimer (125 ng)
x µl
Rückwärtsprimer (125 ng)
x µl
AccuPrimeTM Pfx-Polymerase
0,5 µl
DNA (50 – 50 ng)
x µl
ddH2O.
x µl
Die PCR wurde unter folgenden Bedingungen durchgeführt:
10 min
95 °C
-------------------------------------------------
30 sec
95 °C
1 min
55 °C
1 min/kb
68 °C
x Zyklen
---------------------------------------------------
10 min
68 °C
Bei Punktmutationen wurden 12 Zyklen, bei einem Aminosäureaustausch 16 und bei
Deletionen oder Insertionen von mehreren Nukleotiden wurden 18 Zyklen durchgeführt.
Anschließend wurde 1 µl des Restriktionsenzyms DpnI dazugegeben, um die methylierte
parentale DNA zu verdauen. Die amplifizierte, unmethylierte DNA wurde hingegen nicht
degradiert. Nach 1-stündiger Inkubation bei 37°C wurde 1 µl des Ligationsansatzes zu 50 µl
E
49
Material und Methoden
XL1-Blue gegeben, 30 Minuten auf Eis inkubiert und anschließend auf vorgewärmten LBAmp-Platten ausplattiert und über Nacht bei 37°C inkubiert.
3.20.12 Quantitative PCR (qPCR)
Die Organe, aus denen RNA für die qPCR isoliert werden, sollte wurden nach Entnahme in
RNA Later gelagert. (Für die Homogenisierung des Gewebes siehe Kapitel 3.24.2.2) Die
RNA wurde nach Anleitung des Herstellers isoliert (Macherey-Nagel). Die cDNAHerstellung und die TaqMan RT-PCR erfolgte wie in (215) beschrieben. Total-RNA wurde
aus dem Untersuchungsmaterial extrahiert. Danach wurde mit Hilfe einer Gensonde (Primer)
ein für aviäre Influenzaviren spezifisches Genomstück (RNA) gesucht und mittels des
Enzyms Reverse Transcriptase in cDNA umgeschrieben. Mit Hilfe eines 2. Primers und einer
thermostabilen Taq DNA-Polymerase wurde die umgeschriebene cDNA vermehrt
(amplifiziert). Fragmentlänge des Amplifikates = 100 bp. Das amplifizierte Genomstück
wurde mittels einer innerhalb dieses Genomabschnitts bindenden Sonde nachgewiesen. Eine
gebundene Sonde wurde durch die 5’-3’-Exonukleasefunktion der Taq-DNA-Polymerase
gespalten, worauf der Reporter zu fluoreszieren beginnt. Je früher im Verlauf der PCR die
Fluoreszenz detektierbar ist, desto mehr Virusgenome enthält die Probe. Als Maß dient der
CT-Wert (Cycle of Threshold) (93), der definiert ist als der PCR-Zyklus, bei welchem die
Zunahme der Fluoreszenz einen Cut-Off-Wert (=Threshold) übersteigt. Eine interne PositivKontrolle (IPC) wurde mitgeführt, um die erfolgreiche RNA-Extraktion für jede einzelne
Probe zu überwachen. Fragmentlänge des IPC-Amplifikates = 132 bp. Weitere Referenz:
(80).
Es wurden ca. 1000 RNA-Moleküle pro TaqMan Reaktion beigegeben, was einen CT-Wert
von ca. 28-32 ergeben sollte. Es wurde ein Genomabschnitt aus dem M-Gen nachgewiesen,
eine konservierte Region, die allen Influenza-A-Viren gemeinsam ist.
PCR-Mastermix, alle Proben sowie Kontrollen im Dreifachansatz.
E
50
Material und Methoden
Pro Probe:
H2O (RNase-frei)
6,75 µL
QuantiTect Probe RT-PCR MasterMix
12,50 µL
Primer FLU_panAmod_F (20 µmol/L)
0,50 µL
Primer FLU_panAmod_R (20 µmol/L)
0,50 µL
Probe FLU_panA_P (5 µmol/L)
1,00 µL
Primer EGFP_F (5 µmol/L)
0,50 µL
Primer EGFP_R (5 µmol/L)
0,50 µL
Probe EGFP_P_HEX_BHQ1* (5 µmol/L)
0,50 µL
QuantiTect RT Mix
0,25 µL
RNA aus Probe
2,0 µL
-------25,0 µL
TaqMan laufen lassen. Zyklus-Parameter:
- Reverse Transkription: 48°C (30 Minuten)
- Taq DNA Polymerase Aktivierung: 95°C (10 Minuten)
- PCR: 45 Zyklen: 95°C (15 Sekunden) / 54°C (1 Minute)/ 70°C (1 Minute)
Sense Primer FLU_PanAmod_F, 20 µmol/L (Microsynth): agatgagycttctaaccga
Antisense Primer FLU_PanAmod_R, 20 µmol/L (Microsynth): gcaaagacatcttcaagtytc
TaqMan Sonde FLU_PanA_P, 5 µmol/L (Microsynth): 5’FAM-tcaggccccctcaaagccga3’BHQ1
IPC-spezifische Primer und Sonde:
IPC Sense Primer EGFP_F, 2.5 µmol/L (Microsynth): gaccactaccagcagaacac
IPC Antisense Primer EGFP_R, 2.5 µmol/L (Microsynth): gaactccagcaggaccatg
IPC TaqMan Sonde EGFP_P_HEX_BHQ1*, 5 µmol/L (Microsynth):
5’HEX-agcacccagtccgccctgagca-3’BHQ1
E
51
Material und Methoden
3.21 RNA-Methoden
3.21.1 RNA-Extraktion
Um die Gesamt-RNA von Zellen zu extrahieren, wurden die Zellen in 35 mmGewebekulturschalen ausgesät. Die Zellen wurden zu unterschiedlichen Zeitpunkten nach der
Infektion in 1 ml TriFast (peqLab) bei Raumtemperatur lysiert und anschließend in ein 1,5 ml
Eppendorf-Gefäß überführt. Nach Zugabe von 0,2 ml Chloroform wurde die Lösung
gemischt, 2-3 Minuten bei Raumtemperatur inkubiert und anschließend für 15 Minuten bei
12000×g abzentrifugiert (4°C), wodurch eine deutliche Phasentrennung eintrat. Die obere,
wässrige Phase wurde in ein neues Eppendorf-Gefäß überführt und mit 0,5 ml Isopropanol
vermischt. Das Gemisch wurde für mindestens 1 Stunde bei – 80°C inkubiert um eine
Präzipitation der RNA zu erreichen. Anschließend wurde die RNA durch 20-minütige
Zentrifugation bei 4°C und 12000×g pelletiert. Das RNA-Pellet wurde mit 80 %igem Ethanol
gewaschen, für ungefähr 10 Minuten an Luft getrocknet und schließlich in 30 µl TE-Puffer
gelöst. Die RNA-Konzentration wurde im Spektralphotometer bestimmt und die RNA bei –
20°C gelagert.
3.21.2 cDNA-Synthese
Die Methode wurde angewendet, um cDNA aus RNA mit viralem Ursprung herzustellen. Um
eine Kontamination mit chromosomaler DNA zu vermeiden, wurde 1 µg RNA mit DNase I
(Fermentas) inkubiert. Die Reaktion wurde wie folgt angesetzt und auf 10 µl mit ddH2O
aufgefüllt:
1 µl
10×DNase I Reaktionspuffer
x µl
gereinigte RNA (1 µg)
1 µl
DNase I (1 U)
add 10 ml ddH2O
Die Reaktion wurden nach 30-minütiger Inkubation bei 37°C durch Zugabe von 1 µl 25 mM
EDTA und anschließender Erhitzung auf 65°C für 10 Minuten beendet. 1 µl (200 ng) Random
Hexanucleotide Primers (Gibco) wurden hinzugefügt und konnten an die RNA durch
Inkubation für 5 Minuten bei 70°C binden. Dem folgte eine 10-minütige Inkubation bei
Raumtemperatur. Anschließend wurden die folgenden Komponenten für die Produktion von
cDNA mit Hilfe der RevertAidTM H Minus M-MuLV Reverse Transcriptase hinzugefügt:
E
52
Material und Methoden
4 µl
5×M-MuLV RT Reaktionspuffer
2 µl
dNTP-Mix (10 mM)
1 µl
RNase Inhibitor (40 U)
1 µl
RevertAidTM H Minus M-MuLV Reverse Transcriptase (200 U)
Nach 10-minütiger Inkubation bei Raumtemperatur, wurde die cDNA-Synthese bei 42°C für
1 Stunde durchgeführt und durch Erhitzung auf 70°C für 10 Minuten beendet. Die cDNAProben wurden bei -20°C gelagert.
3.21.3 Northern Blot
3.21.3.1 Präparation der RNA-Proben und Gelelektrophorese
Die gewünschte RNA-Menge wurde in der Vakuum-Zentrifuge getrocknet und danach in
20 µl Ladepuffer aufgenommen. Die RNA-Proben wurden anschließend für 5 Minuten bei
65°C denaturiert, sofort auf Eis abgekühlt und auf ein denaturierendes 1,2%iges Agarosegel
aufgetragen. Die Auftrennung bei 200 V erfolgte bis die RNA-Proben in das Agarosegel
eingelaufen waren, nach dem Anschalten der Umwälzpumpe bei 180 V für 1,5-2 Stunden.
3.21.3.2 Transfer der RNA
Nach ausreichender Auftrennung der RNA im Agarosegel wurde der Gellauf gestoppt. Das
Agarosegel wurde aus der Laufkammer herausgenommen und bei Bestrahlung mit UV-Licht
(260 nm) fotografiert, um sicherzugehen, dass in jede Tasche die gleiche RNA-Menge
geladen wurde. Überflüssige Gel-Masse wurde abgetrennt. Das Gel wurde anschließend für
etwa 30 Minuten in 20×SSC eingelegt. Zum Transfer der RNA aus dem Gel auf eine positiv
geladene Nylon Membran (Nytran N) wurde diese zuvor kurz in Wasser gegeben und
nachfolgend mit 2×SSC äquilibriert. Der Transfer mittels Kapillarkräften erfolgte über Nacht.
Das Gel wurde hierfür auf mit 10×SSC durchtränkte Whatman-Papiere gelegt und mit der
äquilibrierten Nylon-Membran bedeckt. Um eine ausreichende Saugkraft zu gewährleisten,
schloss sich hierauf eine Schicht von drei Whatman-Papieren an. Darauf wurde ein Stapel
Papierhandtücher platziert und beschwert.
Nach dem Transfer wurde die RNA auf der Membran fixiert, in dem diese für mindestens
2 Stunden bei 80°C im Ofen inkubiert wurde.
E
53
Material und Methoden
3.21.3.3 Herstellung einer radioaktiven DNA-Sonde
100 ng der für die Sonde zu verwendenden DNA wurden mit sterilem Wasser auf ein
Gesamtvolumen von 24 µl eingestellt und nach Zugabe von 10 µl Random-OligonukleotidPrimer 5 Minuten bei 95°C erhitzt. Nach sofortiger Abkühlung der Proben auf Eis wurden
10 µl 5×dCTP Primer-Puffer (enthält dATP, dGTP und dTTP), 5 µl radioaktiv markierter
α[32P]dCTP (3000 Ci/mM) und 1 µl Exo(-)Klenow-Polymerase (5 U/µl) dazu pipettiert. Die
Synthese der radioaktiv markierten Sonde erfolgte bei 37°C. Diese Reaktion wurde nach
10 Minuten durch die Zugabe von 2 µl Stopp-Puffer unterbrochen.
Eine chromatographische Auftrennung diente zur Separation der radioaktiven DNA-Probe
von den nicht eingebauten Nukleotiden.
3.21.3.4 Hybridisierung
Die Nylon-Membran wurde für 10 Minuten bei 68°C in 0,2×SSC/0,5%SDS vorbehandelt und
anschließend in eine Hybridisierungsröhre gegeben. Die Prähybridisierung erfolgt in 10 ml
Hybridisierungslösung für etwa 2-3 Stunden bei 42°C und konstanter Rotation im
Hybridisierungsofen.
Vor der Zugabe der Hybridisierungssonde wurde diese für 5 Minuten bei 95°C denaturiert
und auf Eis abgekühlt. Die Hybridisierung wurde über Nacht bei 42°C und konstanter
Rotation durchgeführt. Im Anschluss daran fand die Waschung der Membran zuerst
5 Minuten bei Raumtemperatur, danach 1 Stunde bei 68°C in 2×SSC/0,5%SDS statt, worauf
sich eine Exposition gegen Röntgenfilme anschloss.
3.22 Mikrobiologische Methoden
3.22.1 Herstellung kompetenter Bakterien
Die Herstellung kompetenter Bakterienzellen wurde nach dem vom Hersteller empfohlenen
Protokoll durchgeführt (Z-Competent E. coli Transformation Kit und Buffer Set™, Zymo
Research, USA). 50 ml SOB-Medium wurden mit 500 µl einer E.coli-Übernachtkultur
angeimpft und bei Raumtemperatur und 200 rpm auf einem Horizontalschüttler inkubiert, bis
die OD (optische Dichte)600 einen Wert von 0,4-0,6 erreicht hat. Anschließend wurden die
Bakterien 10 Minuten auf Eis inkubiert und anschließend durch 6-minütige Zentrifugation bei
2500×g und 4°C pelletiert. Der Überstand wurde verworfen, das Pellet wurde in 5 ml
eiskaltem Waschpuffer resuspendiert und wiederum durch 6-minütige Zentrifugation
E
54
Material und Methoden
pelletiert. Zuletzt wurde das Pellet in 5 ml eiskaltem Kompetenzpuffer resuspendiert,
aliquotiert und bei -80°C gelagert.
3.22.2 Transformation von Bakterien
Für die Plasmidpräparation wurden Z-kompetente XL1-Blue- beziehungsweise DH10B- und
chemisch
kompetente
OneShot®TOP10
verwendet.
Bei
den
Z-kompetenten
Bakterienstämmen wurden 100 ng Plasmid in 25 µl Bakteriensuspension gegeben und
30 Minuten auf Eis inkubiert. Anschließend wurde die Suspension auf LB-Agarplatten, die
mit den entsprechenden Antibiotika versetzt waren ausplattiert und über Nacht bei 37°C
inkubiert.
Bei der Plasmidpräparation mittels OneShot®TOP10 erfolgte die Transformation nach
Angaben des Herstellers. Hierbei wurden 100 ng Plasmid zu einem Aliquot OneShot®TOP10
gegeben und diese 15 Minuten auf Eis inkubiert. Nach 2-minütigem Hitzeschock bei 42°C
wurden die Zellen erneut kurz auf Eis inkubiert. Anschließend wurde 100 µl S.O.C. Medium
dazugegeben und bei 37°C 1 Stunde bei 200 rpm auf einem Horizontalschüttler inkubiert.
Zuletzt wurde das Aliquot auf vorgewärmten LB-Platten mit dem jeweiligen Antibiotikum
ausplattiert und diese über Nacht bei 37°C inkubiert.
3.22.3 Kultivierung von Bakterien
Transformierte Bakterien wurden in flüssigem LB-Medium mit 100 µg/ml Ampicillin über
Nacht in einem Horizontalschüttler bei 200 rpm und 37°C kultiviert.
3.23 Proteinbiochemische Methoden
3.23.1 Herstellung von Zelllysaten für Western Blot
Adhärente Zellen wurden in 6-Loch-Platten mit PBS gewaschen, mit 100 µl Lysepuffer
bedeckt und für 10 Minuten auf Eis inkubiert. Dann wurden die Zellen mit einem Zellschaber
vollständig gelöst, in ein Eppendorf-Gefäß überführt und für weitere 10 Minuten auf Eis
inkubiert. Die Lagerung der Lysate erfolgte bei -20°C.
E
55
Material und Methoden
3.23.2 Proteinelektrophorese im SDS-Polyacrylamidgel
Zur elektrophoretischen Auftrennung der Proteine nach ihrem Molekulargewicht wurde die
Methode nach Lämmli (126) angewendet. Dazu wurden ein 10%iges Trenngel und ein
5%iges Sammelgel verwendet. Vor dem Auftragen wurden die Proteine für 5 Minuten bei
95°C in Lämmli-Probenpuffer denaturiert und in einer Mini-Proteinkammer in 4×Laufpuffer
bei 120 Volt für etwa 1 Stunde aufgetrennt.
3.23.3. Western-Blot
Um die elektrophoretisch aufgetrennten Protein nachzuweisen, wurden diese mit Hilfe einer
Elektroblotting-Apparatur auf eine Polyvinyl-Fluorid (PVDF)-Membran transferiert. Das Gel
wurde hierfür auf eine entsprechend große Membran aufgelegt, die zuvor mit Methanol
aktiviert und in Transferpuffer äquilibriert worden war. Gel und Membran wurden daraufhin
zwischen zwei mit Transferpuffer getränkte Whatman-Papiere und Schwämmchen gelegt. Der
Aufbau wurde so in die Apparatur eingebracht, dass die negativ geladenen Proteine in
Richtung der Anode auf die Membran transferiert wurden. Der Transfer fand für 1 Stunde bei
300 mA unter ständiger Kühlung statt.
Anschließend wurde die Membran über Nacht in PBS mit 4% SlimFast geblockt. Nach dem
Blocken
wurde
die
Membran
mit
geeigneter
Verdünnung
eines
spezifischen
Primärantikörpers in PBS mit 0,1% Tween20 und 1% SlimFast für 1 Stunde bei
Raumtemperatur inkubiert. Nach dreimaligem Waschen mit PBS mit 0,1% Tween20 wurden
die Antigen-Antikörper-Komplexe mit einer geeigneten Verdünnung eines HRP-gekoppelten
Anti-IgG-Antikörpers in PBS mit 0,1% Tween20 inkubiert. Die Detektion der gebundenen
HRP-gekoppelten Antikörper erfolgte mit ECL-Reagenz nach Anleitung des Herstellers
(Amersham Bioscience).
3.23.4. IFN-β-ELISA
Zur Quantifizierung des IFN-β in Lungengeweben infizierter Mäuse wurden die Lungen
24 Stunden nach Infektion entnommen und in flüssigem Stickstoff eingefroren. Danach
wurden die Lungen mit Hilfe des FastPrep®-24-Gerätes wie in 3.24.1.2 beschrieben
homogenisiert.
Anschließend
wurden
die
Proben
abzentrifugiert.
Das
in
den
Lungenhomogenaten enthaltene Virus wurde wie unter 3.19.8 beschrieben inaktiviert. Zur
Messung des IFN-β-Gehalts wurde das „Mouse IFN-β ELISA Kit“ von PBL Biochemical
Laboratories entsprechend den Angaben des Herstellers verwendet.
E
56
Material und Methoden
3.23.5. Influenza-A-Virus-Nukleoprotein-basierter ELISA
Zur Quantifizierung des Nukleoproteins in den Lungengeweben infizierter Hühner wurden die
Lungen zu den jeweiligen Zeitpunkten nach der Infektion entnommen und in flüssigem
Stickstoff eingefroren. Danach wurden die Lungen mit Hilfe des TissueLyser II wie in
3.24.2.2 homogenisiert. Anschließend wurden die Proben abzentrifugiert. Die Menge des in
den Lungenhomogenaten vorhandenen NP-Antigens wurde nach Anleitung des Herstellers
(ID Vet) mit Hilfe des „ID Screen® Influenza A Antibody Competition ELISA Kits“
gemessen.
3.23.6. Immunhistochemische Färbung
Von allen Hühnern wurde ein Teil der Lunge in 4% Formaldehyd gegeben und anschließend
in Paraffin eingebettet. Um die Verteilung des Influenza-A-Antigens zu bestimmen, wurden
die Schnitte auf positiv geladene SuperFrost Plus Mikroskopiedeckgläser gelegt (Menzel,
Braunschweig), entparaffinisiert und die endogener Peroxidase wurde durch 3% H2O2 in 90%
Methanol inaktiviert. Die Schnitte wurden 2x 5 Minuten in der Mikrowelle bei 600 Watt in
20mM Citratpuffer (pH 6) erhitzt. Nachdem der unspezifische Hintergrund mit Ziegenserum
geblockt wurde (30 Minuten bei Raumtemperatur) wurden die Schnitte mit Kaninchen-antiNP-Serum inkubiert (Riems). Der Antikörper wurde in einer Verdünnung von 1:750 in TBS
(TRIS-buffered saline) verwendet. Ein biotinylierter Ziegen-anti-Kaninchen IgG1 (Vector,
Burlinghame, CA; 1:200 in TBS) wurde für die ABC-Methode (avidin-biotin-complex) nach
Anleitung des Herstellers eingesetzt. Das braune intrazytoplasmatische und nukleäre Signal
wurde durch ein Immunperoxidase-Kit (Vectastain Elite ABC Kit, Vector) und das Substrat
3-amino-9-ethylcarbazole (DAKO AEC substrate-chromogen system; Dako, Carpinteria, CA,
USA) generiert. Zum Abstoppen der Farbreaktion wurden die Objektträger in Leitungswasser
getaucht. Die Gegenfärbung mit Mayers Hämalaun erfolgte nur etwa 8-10 Sekunden, bevor
die Schnitte für 5 Minuten unter fließendem Leitungswasser gewaschen wurden. In einer
steigenden Alkoholreihe wurden sie anschließend dehydriert und nach mindestens 30minütiger Inkubation in Xylol mit Entelan eingebettet.
3.23.7 Hühner-Interferon-Aufreinigung aus E.coli
Rekombinantes Hühner-IFN-α wurde wie in (201) beschrieben hergestellt. E. coli-Bakterien
des BL-21-Stammes wurden mit dem entsprechenden Expressionsplasmid transformiert. Eine
einzelne Kolonie wurde in 10 ml LB/Ampicillin (100 µg/ml) angeimpft und über Nacht bei
E
57
Material und Methoden
37°C im Schüttler inkubiert. Anschließend wurde diese 10 ml-Übernachtkultur zu 1 l
LB/Ampicillin, das mit 20 mM Glucose versetzt war, gegeben und bis zu einer OD600 von
0,3-0,5 wachsen gelassen. Die Proteinexpression des rekombinanten Proteins wurde durch
Zugabe von 0,5 mM IPTG induziert. Danach wurde die Kultur für weitere 2 Stunden bei 37°C
inkubiert und schließlich für 30 Minuten bei 4°C und 4000 rpm abzentrifugiert. Das Pellet
wurde in 10 ml „Ultraschallbehandlungs-Puffer“ resuspendiert und für 30 Sekunden im
Eiswasser beschallt. Anschließend wurden die Proben für 30 Sekunden auf Eis inkubiert,
damit die Wärmeentwicklung bei der Ultraschallbehandlung nicht zu groß wurde. Das ganze
wurde 6x wiederholt. Danach wurden die Proben für 25 Minuten bei 12000 rpm zentrifugiert
und der Überstand wurde verworfen. Das Pellet wurde in 10 ml „Puffer A“ resuspendiert und
bei Raumtemperatur für 2 Stunden inkubiert. Anschließend wurde erneut für 30 Minuten bei
12000 rpm zentrifugiert. In der Zwischenzeit wurden 5 ml 50%-Nickel-Agarose mit 15 ml
ddH2O gewaschen und für 3 Minuten bei 500 rpm zentrifugiert. Die Agarose wurde dann mit
40 ml „Puffer A“ äquilibriert und wiederum für 3 Minuten bei 500 rpm zentrifugiert.
Anschließend wurde das Proteinlysat mit der Nickel-Agarose auf einem Überkopfschüttler
über Nacht bei 4°C inkubiert. Die wässrige Masse wurde am nächsten Tag auf leere PD-10Säule gegeben und zuerst mit 50 ml „Puffer A“ und dann mit 25 ml „Puffer B“ gewaschen.
Danach wurde „Puffer B“ schrittweise durch „Puffer B’“ mit Hilfe einer peristaltischen
Pumpe ausgetauscht. Nach erneutem Waschen mit 25 ml „Puffer B’“ und 25 ml „Puffer E I“
wurde das Protein mit Hilfe eines linearen Gradienten von „Puffer II“ in 10 ml eluiert. Die
ersten 6 - 7 ml wurden in einem Falcon-Gefäß aufgefangen, der Rest in 2 ml-EppendorfGefäßen. Die Quantität und Qualität des aufgereinigten Proteins wurde mit Hilfe eines SDSGels überprüft. Als Kontrolle wurde auch Bakterienlysat vor und nach der Induktion mit
IPTG, Proteinlysat vor der Inkubation mit der Ni2+.-Agarose, der Durchfluss und alle
gesammelten Fraktionen auf ein SDS-Gel geladen.
3.24 Tierexperimentelle Methoden
3.24.1. Mausexperimente
3.24.1.1 Infektion der Versuchstiere
Die Versuchstiere wurden intranasal mit 50 µl einer Virussuspension inokuliert. Das Virus
wurde dazu in PBS auf die gewünschte Infektionsdosis verdünnt. Vor Infektion wurden die
E
58
Material und Methoden
Tiere durch intraperitoneale Injektion von 10 µl der unter 3.10.6 beschriebenen Rezeptur pro
Gramm Körpergewicht anästhesiert.
Bei einem Gewichtsverlust von mehr als 25% oder deutlichen Krankheitsanzeichen wie einem
stark gekrümmten Rücken, struppigem Fell, trockenen Augen und Apathie wurden die Tiere
euthanasiert. In allen Experimenten wurden sechs bis acht Wochen alte Mäuse eingesetzt.
3.24.1.2 Herstellung von Organhomogenaten
Für die Bestimmung des Virustiters und des FN-Gehalts in den Lungen wurden diese nach
Entnahme in ein 2ml-Mikro-Schraubröhrchen gegeben. Danach wurde 1 ml PBS dazu
gegeben. Das Ganze wurde 2x 15 Sekunden bei 6,5 m/s in einem FastPrep®-24
homogenisiert. Dazwischen wurden die Proben auf Eis gekühlt. Nach der Homogenisierung
wurden die Proben bei 4°C und 3500 rpm für 10 Minuten zentrifugiert. Der Überstand wurde
in ein neues Eppendorf-Gefäß überführt und für die weitere Verwendung auf -80°C gefroren.
3.24.2 Hühnerexperimente
Für die Experimente wurden SPS (specific pathogen free)-Hühner (LSL, Lohmann selected
Leghorn) von der Firma Lohmann Tierzucht GmbH in Cuxhaven verwendet. In allen
Experimenten wurden drei bis fünf Wochen alte Hühner eingesetzt.
3.24.2.1 Infektion der Versuchstiere
4-7 Hühner/Gruppe wurden intratracheal mit 1x106ffu (SC35-Experimente) beziehungsweise
6x105ffu (R65-Experimente) unter Verwendung einer stumpfen Kanüle infiziert. Das Virus
wurde dazu in PBS auf die gewünschte Infektionsdosis mit einem Endvolumen von 300µl in
PBS verdünnt. 12, 24 und 72 Stunden nach Infektion wurde je eine Gruppe geschlachtet und
Lunge, Milz und Gehirn wurden für die Virustitration und den IFN-Bioassay entnommen.
Außerdem wurde vor der Schlachtung Blut entnommen, um Plasma für den IFN-Assay
herzustellen. Alle 12 Stunden wurden Kloaken- beziehungsweise Pharynxtupfer genommen
und in Virusisolationsmedium für 30 Minuten bei Raumtemperatur geschüttelt und
anschließend bei -80°C bis zur weiteren Verwendung gelagert.
E
59
Material und Methoden
3.24.2.2 Herstellung von Organhomogenaten
Für die Bestimmung des Virustiters und des IFN-Gehalts in den Organen der Hühner wurden
diese nach Entnahme in ein 2ml-Eppendorf-Gefäße gegeben und sofort in flüssigen Stickstoff
Schock-gefroren. Für die Organhomogenate wurden anschließend kleine Stücke der Organe
mit einer Schere abgetrennt und gewogen. Dann wurde 1 ml PBS dazu gegeben und das
Ganze wurde für 2x 30 Sekunden mit einem TissueLyser II homogenisiert. Gewebereste
wurden durch langsame Zentrifugation bei 4°C entfernt und der Überstand wurde in ein neues
Eppendorf-Gefäß überführt und bei -80°C für die weiterer Verwendung eingefroren. Für die
RNA-Isolierung wurde das Gewebestück in Trizol homogenisiert.
E
60
Ergebnisse
4. Ergebnisse
4.1 Wachstumsverhalten und Interferon-Induktion von SC35-wt (H7N7)
und Mutanten in Zellkultur und verschiedenen in vivo-Systemen
Im Rahmen dieser Doktorarbeit sollte das Zusammenwirken von aviären Influenza-A-Viren
mit dem IFN-System des Huhns als natürlichem Wirt näher untersucht werden. Im Gegensatz
zur Maus, die oft als Modellsystem verwendet wird, um die Ausbreitung von Influenza-AViren und die Interaktion mit dem Immunsystem zu untersuchen, ist beim aviären
angeborenen Immunsystem im Zusammenhang mit Influenzaviren noch nicht allzu viel
bekannt. Um die Rolle des NS1-Proteins als IFN-Antagonist im Huhn zu untersuchen, wurde
ein Influenza-A-Virus-Stamm vom Typ H7N7 (A/seal/Mass/1/80) verwendet. Dieser Stamm,
der 1980 während eines Ausbruchs von akuter hämorrhagischer Pneumonie unter Seehunden
an der Küste Neu-Englands isoliert wurde, weist große Ähnlichkeiten mit natürlich
vorkommenden, zirkulierenden aviären Influenzaviren auf. Allerdings wurde gezeigt, dass
dieses Virus relativ gut in Schweinen, Frettchen und Katzen repliziert, jedoch nur sehr
schlecht in aviären Spezies (8, 255, 256). Deshalb wurden Adaptationsstudien durchgeführt,
bei denen das Virus 35x in Hühnerzellen passagiert wurde. Dabei wurden verschiedene
Punktmutationen und eine multibasische Spaltstelle im HA generiert, wodurch SC35
pathogen für Hühner wurde (132). Die bidirektionalen Plasmide mit den entsprechenden
Sequenzen
für
die
Generierung
der
rekombinanten
SC35-Viren
Kooperationspartnern der Insel Riems zur Verfügung gestellt.
AS 73 AS 153
NS1 1-73-Gen
650nt
NS1 1-73-mRNA
73AS
NEP mRNA
121AS
wt NS-Gen
890nt
wt-NS1 mRNA
230AS
NEP mRNA
121AS
AAA
AAA
AAA
AS 99
AAA
AAA
AAA
AS 126 AS 153
AAA
NS1 1-126-Gen
809nt
NS1 1-126-mRNA
126AS
NEP mRNA
121AS
Abbildung 4.1: Verwendete NS1-Konstrukte für den Rescue der SC35-Viren
AS = Aminosäure; nt = Nukleotid
AS 153
NS1 1-99-Gen
728nt
NS1 1-99-mRNA
99AS
NEP mRNA
121AS
AS 10 AS 165
delNS1-Gen
425nt
delNS1-mRNA
10AS
NEP mRNA
121AS
AAA
AAA
AAA
wurden
von
E
61
Ergebnisse
Mit Hilfe des 12-Plasmid-Systems wurden rekombinantes SC35-wt und verschiedene NS1Mutanten
generiert.
Deren
NS1
besaß
73
[SC35-NS1(73)],
99
[SC35-NS1(99)]
beziehungsweise 126 N-terminale Aminosäuren [SC35-NS1(126)]. Des Weiteren wurde eine
Mutante generiert, welcher der komplette NS1-ORF fehlte (SC35-delNS1) (Abbildung 4.1).
Für die Herstellung dieser rekombinanten Viren wurde eine Kokultur aus 293T- und MDCKNS1-GFP-Zellen verwendet. Letztere exprimieren stabil ein NS1-GFP-Fusionsprotein und
unterstützen so die Generierung von Mutanten mit NS1-Defekten. Bei allen NS1-Mutanten
war durch die eingefügten Deletionen die Expression des NEP-Proteins nicht betroffen. Wie
aus Tabelle 4.1 ersichtlich ist, waren alle Rescues erfolgreich. Die korrekte Sequenz des NS1kodierenden 8. Segments wurde bei allen Viren durch Sequenzanalysen bestätigt.
Name
Merkmal
Rescue
SC35-wt
8 Segmente von SC35
+
SC35-NS1(73)
7 Segmente von SC35, 8. Segment besitzt NS1-Protein mit 73 Nterminalen Aminosäuren + NEP-Protein von SC35
+
SC35-NS1(99)
7 Segmente von SC35, 8. Segment besitzt NS1-Protein mit 99 Nterminalen Aminosäuren + NEP-Protein von SC35
+
SC35-NS1(126)
7 Segmente von SC35, 8. Segment besitzt NS1-Protein mit 126 Nterminalen Aminosäuren + NEP-Protein von SC35
+
SC35-delNS1
7 Segmente von SC35, besitzt kein NS1-Protein, aber NEPProtein von SC35
+
Tabelle 4.1: Tabelle der generierten rekombinanten SC35-Viren
4.1.1 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten SC35-Viren in Hühnerzellen
Da aus der Literatur bekannt ist, dass Viren mit C-terminalen Deletionen im NS1-Protein in
IFN-kompetenten Zellen prinzipiell weniger gut replizieren (68), sollten die generierten Viren
zu allererst auf ihr Wachstumsverhalten in aviären Zellen untersucht werden. Dafür wurden
Hühnerembryo-Fibroblasten (CEFs) mit einer geringen MOI infiziert. Das Ergebnis ist in
Abbildung 4.2 dargestellt. SC35-wt replizierte sehr gut und wuchs bis Titer von ca.
107 ffu/ml.
Die
C-terminal
verkürzten
NS1-Mutanten
zeigten
ein
ähnliches
Wachstumsverhalten. Auch für andere Influenza-A-Stämme mit C-terminal verkürzten NS1Proteinen ist bereits gezeigt worden, dass sie in IFN-kompetenten Zellen bis zu einem
gewissen Grad replizieren können (40, 115). Nur SC35-delNS1 war deutlich attenuiert.
Allerdings war diese Mutante dennoch in der Lage, bis zu Titern von ca. 1x104 ffu/m zu
E
62
Ergebnisse
wachsen. Die Tatsache, dass SC35-delNS1 überhaupt in der Lage war, in CEFs zu wachsen
war sehr überraschend, da diese Virusmutante keinen IFN-Antagonisten besitzt und diese
Virustiter
[log10 (ffu/ml)]
Zellen über ein aktives IFN-System verfügen.
8
6
SC35-wt
SC35-NS1(73)
SC35-NS1(99)
SC35-NS1(126)
SC35-delNS1
4
2
0
0
12
24
36
48
60
Zeit (h nach Infektion)
Abbildung 4.2: Wachstumsverhalten von SC35-wt und den SC35-Mutanten in Hühnerzellen
Semi-konfluente CEFs wurden mit SC35-wt (gefüllte Kreise), SC35-NS1(73) (Quadrate), SC35-NS1(99) (gefüllte Dreiecke),
SC35-NS1(126) (Diamanten) beziehungsweise SC355-delNS1 (gefüllte Dreiecke) mit einer MOI von 0,001 infiziert. Die
Virustiter im Zellkulturüberstand wurden an den angegebenen Zeitpunkten bestimmt. Das Ergebnis von drei unabhängigen
Experimenten ist dargestellt.
Das NS1-Protein fungiert als IFN-Antagonist und ist in der Lage, die angeborene
Immunantwort zu inhibieren (68). Deshalb sollte als nächstes untersucht werden, ob die
generierten SC35-Viren in der Lage sind, die IFN-Produktion in aviären Zellen zu
unterdrücken. Zuerst wurde mittels RT-PCR die Induktion der IFN-β-Transkripte analysiert.
Dazu wurden CEFs mit einer MOI von 0,5 der entsprechenden Viren infiziert und 10 Stunden
nach Infektion wurde die RNA isoliert und eine RT-PCR für IFN-β durchgeführt. Als
Kontrollen wurden NP-, NS1- und Aktin-Transkripte verwendet. Wie in Abbildung 4.3 zu
erkennen ist, induzierte SC35-delNS1 als einziges Virus eine große Menge an IFN-β-mRNA.
Weder SC35-wt noch die C-terminal verkürzten NS1-Mutanten induzierten eine detektierbare
NS
1(7
3)
35
-N
S1
SC
(99
35
)
-N
S1
SC
(12
35
6)
-de
lN
mo
S1
ck
SC
35
-
SC
SC
35
-w
t
Menge an IFN.
IFNβ
SC35-NS1
SC35-NP
β-Actin
Abbildung 4.3: IFN-Induktion von SC35-wt und den SC35-Mutanten in Hühnerzellen
Konfluente CEFs wurden mit den verschiedenen Viren mit einer MOI von 0,5 infiziert und 10 Stunden nach Infektion wurde
die IFN-Induktion mittels RT-PCR bestimmt. Ein repräsentatives Ergebnis ist dargestellt.
E
63
Ergebnisse
Da CEFs nach einer Influenza-A-Infektion hauptsächlich IFN-α produzieren (203) und mit
Hilfe der RT-PCR nur die IFN-β-Transkripte detektiert wurden, wurde zusätzlich die
Anwesenheit von biologisch aktivem IFN im Überstand überprüft. Der dazu verwendete
Bioassay, der in Abbildung 4.4 schematisch dargestellt ist, basiert auf einer aviären
Reporterzelllinie (CEC-32#511), die als Reportergen Luziferase unter Kontrolle des aviären,
IFN-induzierbaren Mx-Promotors exprimiert (203). Sobald der Hühner-Mx-Promotor in
diesen Zellen durch das IFN aktiviert wird, kommt es zur Expression der Luziferase, deren
Aktivität anschließend im Luminometer gemessen werden kann und die mit der Menge an
IFN korreliert.
IFN
IFNAR
Hühner-Mx-P
4
Luziferase
3
?
Firefly-Luziferase-Aktivität ?
Abbildung 4.4: Schematische Darstellung des Luziferase-Reporter-Assays zur Detektierung von aviärem Typ I IFN
CEC-32-Zellen exprimieren stabil das Luziferasegen unter Kontrolle des Hühner-Mx-Promotors. Die Behandlung der
Indikatorzellen mit aviärem Typ I IFN führt über die Bindung an den Typ I IFN-Rezeptor zur Auslösung der JAK/STATSignalkaskade und somit zur Aktivierung des Mx-Promotors. Dadurch wird die Luziferase-Expression induziert. Die
Luziferase-Aktivität im Zelllysat wird anschließend im Luminometer gemessen.
Um zu untersuchen, ob die verschiedenen SC35-Viren die IFN-Produktion inhibieren können,
wurden deshalb CEFs mit einer MOI von 0,5 infiziert und 24 Stunden nach Infektion wurde
die IFN-Menge im Überstand mit Hilfe der Indikatorzellen bestimmt. In Abbildung 4.5 ist
sehr gut zu sehen, dass SC35-wt in der Lage war, die IFN-Produktion zu inhibieren, während
SC35-delNS1 große Mengen an Hühner-IFN induzierte. Bei diesem Assay sieht man deutlich,
dass die C-terminalen NS1-Mutanten mehr IFN als SC35-wt induzierten, aber deutlich
weniger als die Virusmutante, die kein NS1 exprimiert.
E
Ergebnisse
200
150
100
50
oc
k
m
SC
35
-w
t
-N
S1
SC
(7
3)
35
-N
S1
SC
(9
35
9)
-N
S1
(1
SC
26
)
35
-d
el
N
S1
0
SC
35
Hühner-IFN (Units/ml)
64
Abbildung 4.5: IFN-Induktion von SC35-wt und den SC35-Mutanten in Hühnerzellen
Konfluente CEFs wurden mit einer MOI von 0,5 infiziert und nach 24 Stunden mittels Bioassay auf IFN-Aktivität im
Überstand untersucht. Das Ergebnis von drei unabhängigen Experimenten ist dargestellt.
Für andere Virusstämme wurde bereits gezeigt, dass eventuell vorhandene Viren in den
Zellkulturüberständen kein IFN in diesen Indikatorzellen induzieren. Es wird angenommen,
dass diese Zellen einen Defekt in einer der Signalkaskaden haben, die normalerweise durch
Viren aktiviert werden. Um zu überprüfen, ob das auch für den in dieser Arbeit verwendeten
Virusstamm SC35 gilt, wurden CEC-32#511-Reporterzellen mit SC35-wt, aber auch mit der
Mutante, die eine Deletion des NS1-ORFs enthielt, infiziert. Letztere wurde verwendet, weil
das Vollängen-NS1-Protein die IFN-Produktion inhibieren könnte (68). Die Zellen wurden
deshalb für 1 Stunde infiziert und anschließend gewaschen und mit normalem Medium
inkubiert. Nach 6 Stunden wurden die Zellen lysiert und die Luziferase-Aktivität gemessen.
Wie in Abbildung 4.6 zu erkennen ist, induzierte weder SC35-wt noch SC35-delNS1 eine
nennenswerte Menge an IFN. Damit konnte eine direkte IFN-Induktion durch Viruspartikel in
Hühner-IFN (Units/ml)
den Reporterzellen des Bioassays ausgeschlossen werden.
6
SC35-wt
6
4
4
2
2
0
106 105 104 103 102 10
1 10-1 10-2 10-3 10-4 10-5 10-6 mock
ffu
0
SC35-delNS1
106 105 104 103 102 10
1 10-1 10-2 10-3 10-4 10-5 10-6 mock
ffu
Abbildung 4.6: Test der CEC-32#511-Zellen auf IFN-Induktion nach Infektion mit SC35-wt und SC35-delNS1.
CEC-32-Zellen, die stabil mit einem Plasmid (#511), welches das Luziferasegen unter Kontrolle des Hühner-Mx-Promotors
trägt, transfiziert waren, wurden für 1 Stunde mit den angegebenen Virusdosen von SC35-wt (linke Abbildung) und SC35delNS1 (rechte Abbildung) infiziert. Nach 6-stündiger Inkubation mit Medium wurden die Zellen lysiert und die LuziferaseAktivität wurde bestimmt. Anhand eines IFN-Standards wurde die Luziferase-Aktivität in IFN-Units umgerechnet.
E
65
Ergebnisse
4.1.2 Herstellung von Trachealorgankulturen als ex vivo-System
Um dem aviären in vivo-System näher zu kommen, wurde ein ex vivo-System etabliert, das
auf Trachealorgankulturen (TOCs) von 19 Tage alten Hühnerembryonen basierte. Dazu
wurde die Trachea aus dem Embryo präpariert und in ca. 0,7 mm-dicke Ringe geschnitten.
Eine solche Kultur ist in Abbildung 4.7 gezeigt. Die TOCs wurden bei 37°C in 5ml-Gefäßen
mit speziellem Medium im Überkopfschüttler inkubiert. Das Überleben der Ringe konnte
anhand der Ziliaraktivität im Inneren des Rings bestimmt werden. Für die Versuche wurden
nur Ringe mit 100%iger Ziliaraktivität eingesetzt.
1,5 mm
Abbildung 4.7: Darstellung eines Trachealrings
Um die IFN-Antwort der TOCs zu überprüfen, wurden diese mit einer hohen Dosis HühnerIFN-α behandelt und nach 8 beziehungsweise 24 Stunden wurde getestet, ob die Expression
von Hühner-Mx induziert wurde. Zuerst wurde aus jeweils drei identisch behandelten Ringen
die RNA isoliert und in cDNA umgeschrieben. Anschließend wurde die Expression der MxmRNA und als Kontrolle der Aktin-mRNA über eine PCR bestimmt. Wie in Abbildung 4.8
zu sehen ist, konnte durch die IFN-Behandlung die Expression der Mx-mRNA induziert
werden. Weiterhin wurde nicht nur die RNA-Induktion, sondern auch die Proteinexpression
nach IFN-Behandlung untersucht. Dafür wurden je drei Ringe in Lysepuffer aufgenommen,
homogenisiert und anschließend im Western-Blot auf Mx-Expression und als Kontrolle auf
Tubulin-Expression getestet. Auch hier war bei den IFN-behandelten TOCs eine prominente
Mx-Bande zu erkennen, die bei den Kontrollen nicht vorhanden war. Das deutet an, dass der
IFN-Signalweg der zur Expression von ISGs führt in den TOCs intakt und funktionell war.
E
66
FN
2
100
0U
I
4h
mo
ck
2
0U
IFN
8
100
mo
ck
8h
h
4h
Ergebnisse
Mx
RT-PCR
γ-Aktin
Mx
Western-Blot
β-Tubulin
Abbildung 4.8: Mx-Expression nach Behandlung der Trachealorgankulturen mit IFN
TOCs wurden mit 1000 Units Hühner-IFN-α für 8 beziehungsweise 24 Stunden behandelt oder in Medium ohne IFN-Zusatz
gehalten. Jeweils drei Ringe wurden auf Mx-mRNA-Induktion mittels RT-PCR getestet (obere Abbildung) während andere
auf Mx-Expression mittels Western-Blot getestet wurden (untere Abbildung). Ein repräsentatives Ergebnis ist dargestellt.
4.1.3 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten SC35-Viren in Trachealorgankulturen
Als nächstes wurden TOCs auf ihre Funktionalität als ex vivo-System für Influenza-A-VirusInfektionen getestet. Dazu wurde die Replikationsfähigkeit von SC35-wt und den Mutanten in
den TOCs untersucht. Je 1 Ring wurde für 1 Stunde mit 100 ffu der entsprechenden Viren
infiziert, gewaschen und mit Medium bei 37°C inkubiert. Alle 12 Stunden wurde ein Aliquot
des Überstandes abgenommen und titriert. Wie Abbildung 4.9 zeigt, wuchs SC35-wt auch in
diesen Organkulturen zu hohen Titern von ca. 1x106 ffu/ml. Die C-terminal verkürzten NS1Mutanten waren auch in der Lage bis zu einem gewissen Grad zu wachsen, allerdings schien
dies nicht in jedem Ring der Fall zu sein. Ein möglicher Grund ist, dass jeder Ring etwas
anders beschaffen und die Zahl an lebenden Zellen unterschiedlich ist. Es scheint einen
Schwellenwert zu gegeben (eine Mindestanzahl an Zellen pro Ring, die initial infiziert sein
müssen), damit das Virus in der Lage ist, gut zu replizieren und sich auszubreiten. Bei SC35delNS1 waren jedoch in keinem Fall Titer im Überstand messbar, obwohl verschiedene
Virusmengen (100 ffu/Ring – 105 ffu/Ring) für die Infektion eingesetzt wurden. Dieses
Ergebnis war überraschend, da SC35-delNS1 in den CEFs in der Lage war, zumindest zu
moderaten Titern zu wachsen, obwohl CEFs nach Virusinfektion IFN produzieren
(Abbildungen 4.3 + 4.5).
E
67
Virustiter
[log10 (ffu/ml)]
8
SC35-wt
Ergebnisse
1.0
SC35-delNS1
0.8
6
0.6
4
0.4
2
0
0.2
0
12
24
36
48
60
0.0
0
Virustiter
[log10 (ffu/ml)]
4
SC35-NS1(73)
4
12
24
36
SC35-NS1(99)
4
3
3
3
2
2
2
1
1
1
0
0
12
24
36
48
60
Zeit (h nach Infektion)
0
0
12
24
48
60
Zeit (h nach Infektion)
Zeit (h nach Infektion)
36
48
60
Zeit (h nach Infektion)
0
SC35-NS1(126)
0
12
24
36
48
60
Zeit (h nach Infektion)
Abbildung 4.9: Wachstumsverhalten von SC35-wt und den SC35-Mutanten in Trachealorgankulturen
TOCs wurden mit 100 ffu/Ring von SC35-wt (linke, obere Abbildung), SC35-delNS1 (rechte, obere Abbildung), SC35NS1(73) (untere, linke Abbildung), SC35-NS1(99) (untere, mittlere Abbildung) beziehungsweise SC35-NS1(126) (untere,
rechte Abbildung) infiziert. Die Virustiter im Zellkulturüberstand wurden an den angegebenen Zeitpunkten bestimmt. Jeder
Punkt stellt einen individuellen Ring dar.
Die nächste Frage war, ob das Replikationsverhalten der verschiedenen SC35-Viren mit der
IFN-Induktion korrelierte. Dazu wurde je ein Ring mit einer hohen Dosis von 104 ffu/ml
infiziert und 24 Stunden nach Infektion wurde der Überstand abgenommen und auf biologisch
aktives IFN mittels Bioassay getestet (Abbildung 4.10). SC35-wt war wie in CEFs in der
Lage, die IFN-Produktion zu inhibieren. Die C-terminal verkürzten NS1-Mutanten
induzierten wiederum eine große Menge an Hühner-IFN. Überraschenderweise war jedoch
SC35-delNS1 kein starker IFN-Induktor wie es in Hühnerzellen der Fall war und wie es laut
Literatur zu erwarten war (68, 114, 115). SC35-delNS1 induzierte kaum mehr IFN als SC35wt. Wahrscheinlich reicht eine geringe Menge an IFN in den TOCs schon aus, um diese
Virusmutante vollständig zu inhibieren. Dieses Ergebnis deutete schon darauf hin, dass es im
Huhn Unterschiede bezüglich der IFN-Antwort in vitro und in vivo gibt.
E
Ergebnisse
1000
800
600
400
200
m
oc
k
0
S
SC C3
35 5-w
-N
t
S1
SC
(
35
73
SC -NS )
1(
35
- N 99)
S
SC 1(1
26
35
)
-d
el
N
S1
Hühner-IFN (Units/ml)
68
Abbildung 4.10: IFN-Induktion von SC35-wt und den SC35-Mutanten in Trachealorgankulturen
TOCs wurden mit 104 ffu/Ring der angegebenen Viren infiziert und nach 24 Stunden mittels Bioassays auf IFN-Aktivität im
Überstand untersucht. Jeder Punkt stellt einen individuellen Ring dar.
4.1.4 Untersuchung der Interferon-Induktion von SC35-wt und SC35-delNS1 in
Luziferase-Reporter-Mäusen
Als nächstes sollte die IFN-Induktion von SC35-wt und SC35-delNS1 in einem in vivoSystem untersucht werden. Da das Mausmodell ein sehr gut etabliertes System ist, um das
Verhalten von Influenzaviren zu untersuchen, wurden als erstes Luziferase-Reporter-Mäuse
infiziert. Diese Reportermäuse besitzen an Stelle des IFN-β-Gens das Luziferasegen unter
Kontrolle des IFN-β-Promotors. Nach Infektion wird deshalb statt IFN-β Luziferase
exprimiert, deren Aktivität nach Homogenisierung der jeweiligen Organe im Luminometer
gemessen werden kann. Es wurde in früheren Studien gezeigt, dass die Luziferase-Expression
in Lungenhomogenaten dieser Tiere mit der induzierten Menge an IFN-β korreliert (134).
Diese Mäuse wurden intranasal mit 5x104 ffu SC35-wt beziehungsweise SC35-delNS1
infiziert und 24 Stunden nach Infektion wurden die Lungen entnommen und die LuziferaseAktivität bestimmt (Abbildung 4.11). Wie erwartet war in den Lungen SC35-wt-infizierter
Mäuse kaum Luziferase-Aktivität messbar, was zeigt, dass dieses Virus auch in diesem
System in der Lage ist, die IFN-Produktion zu inhibieren. SC35-delNS1 hingegen induzierte
eine sehr hohe Luziferase-Aktivität, wie es auch bei anderen NS1-deletierten Influenza-AViren der Fall ist (68, 114).
E
Ergebnisse
8.0×10 5
6.0×10 5
4.0×10 5
2.0×10 5
*
SC
m
oc
k
35
-d
el
N
S1
35
-w
t
0
SC
Luciferase-Aktivität (RLU)
69
Abbildung 4.11: IFN-Induktion von SC35-wt und SC35-delNS1 in Luziferase-Reporter-Mäusen
IFN-β-Luziferase-Mäuse wurden intranasal mit 5x104 ffu SC35-wt beziehungsweise SC35-delNS1 infiziert (n=4/Gruppe).
24 Stunden nach Infektion wurden die Lungen der Mäuse entnommen und die Luziferase-Aktivität im Luminometer
bestimmt. Der Stern markiert die Werte, die unter dem Detektionslimit liegen. (RLU: relative Licht-Units)
4.1.5 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion von
SC35-wt und SC35-delNS1 in adulten Hühnern
Schlussendlich wurden die rekombinanten Viren in ihrem natürlichen Wirt untersucht, um die
Reaktion des aviären IFN-Systems genauer unter die Lupe zu nehmen. Für dieses initiale
Experiment wurden nur SC35-wt und SC35-delNS1 verwendet, da bei diesen beiden Viren,
ausgehend von den vorherigen Ergebnissen, die größten Unterschiede erwartet wurden.
Adulte Hühner wurden mit 1x106 ffu intratracheal infiziert, um anschließend die Replikation
und IFN-Induktion vor allem in der Lunge zu charakterisieren. Die intratracheale Infektion
wurde gewählt, um die Reaktion des IFN-Systems mit dem Mausmodell vergleichen zu
können, obwohl bei einer natürlichen Infektion des Huhns der Nasenrachenraum der primäre
Replikationsort ist (226). Um gleichzeitig auch die Übertragungsfähigkeit von SC35-wt zu
testen, wurden vier Hühner als Sentinels zu der mit SC35-wt infizierten Gruppe zugesetzt.
Aufgrund der bisherigen Ergebnisse wurde angenommen, dass SC35-delNS1 nicht pathogen
genug ist, um übertragen zu werden. Deshalb wurden keine Sentinel-Tiere zu der mit SC35delNS1 infizierten Gruppe gesetzt.
Je eine Gruppe Hühner wurde 10 Tage lange beobachtet und auf Überleben getestet. Bei sehr
auffälligem Krankheitszustand der Tiere wurden diese getötet. In Abbildung 4.12 ist zu sehen,
dass die mit SC35-wt infizierten Hühner spätestens nach 6 Tagen euthanasiert werden
mussten, während die mit SC35-delNS1 infizierten Hühner wie erwartet überlebten. Auch die
Sentinel-Tiere haben diesen Zeitraum überlebt.
E
70
Ergebnisse
Überleben (%)
100
SC35-wt
SC35-delNS1
80
60
40
20
0
0
2
4
6
8
10
Zeit (Tage nach Infektion)
Abbildung 4.12: Überlebenskurven adulter Hühner infiziert mit SC35-wt und SC35-delNS1
Sechs Wochen alte Hühner wurden intratracheal mit 1x106 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe). Der
Zustand der Hühner wurde täglich überprüft. Im Falle von starken Krankheitssymptomen wurden die Tiere getötet.
Um zu untersuchen, ob die Pathogenität der Viren mit der Replikationsfähigkeit
zusammenhängt, wurden Gruppen von je fünf Hühnern nach 20 und 66 Stunden getötet und
Milz und Lunge entnommen. Beide Organe wurden auf Virusreplikation mittels Titration
überprüft. Erstaunlicherweise gelang es nicht, Viren aus den entsprechenden Organen zu
isolieren, obwohl zumindest mit SC35-wt infizierte Tiere große Mengen an Virus aufweisen
müssten. Vermutlich war die Ursache technischer Natur. Die Proben wurden eventuell nicht
schnell genug gekühlt, so dass die Viren in dieser Zeit durch Proteasen oder andere zelluläre
Enzyme degradiert wurden, weshalb keine infektiösen Viruspartikel mehr detektierbar waren.
Um dennoch Aussagen über die Unterschiede in der Virusmenge zwischen den beiden Viren
treffen zu können, wurden qRT-PCR-Analysen auf Basis der viralen Nukleoprotein-RNA
durchgeführt, die sensitiver sind (Abbildung 4.13). SC35-wt wurde in der Lunge der
infizierten Tiere gefunden und auch in der Milz, was auf eine systemische Infektion
hindeutete. SC35-delNS1 hingegen war nur in der Lunge 20 und 66 Stunden nach Infektion
detektierbar, wobei die Menge zu dem späteren Zeitpunkt abnahm. Zuletzt wurde das Virus
vollständig eliminiert. In der Milz war zu keinem Zeitpunkt SC35-delNS1 detektierbar, was
zeigt, dass das Virus zu attenuiert war, um sich ausbreiten zu können. Die Kontrolltiere und
die Sentinels waren zu allen Zeitpunkten negativ.
E
71
50-CT
40
Lunge
30
30
Ergebnisse
Milz
SC35-wt
SC35-delNS1
Sentinels
Kontrollen
20
20
10
10
**
0
** Ende
***
20
66
0
Zeit (h nach Infektion)
** ***
***
66
Ende
20
Zeit (h nach Infektion)
Abbildung 4.13: Wachstumsverhalten von SC35-wt und SC35 delNS1 in adulten Hühnern
Sechs Wochen alte Hühner wurden intratracheal mit 1x106 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe). RNAExpression des viralen NP-Gens in der Lunge (linke Abbildung) und in der Milz (rechte Abbildung) wurden zu den
angegebenen Zeitpunkten bestimmt. Die Sterne markieren Werte, die unter dem Detektionslimit liegen. (Ende: Zeitpunkt der
Euthanasierung für SC35-wt-infizierte Hühner: Tag 4-6; Zeitpunkt der Euthanasierung für SC35-delNS1-infizierte Hühner:
Tag 10; CT = cycle of threshold)
Jeden Tag wurden Kloaken- und Pharynxtupfer genommen und ebenfalls mittels qRT-PCR
auf Virus untersucht (Abbildung 4.14). Die mit SC35-wt infizierten Hühner waren zu allen
Zeitpunkten bis zu ihrem Tod nach 6 Tagen positiv. Wahrscheinlich war die Virusmenge aber
nicht groß genug, als dass es für eine Neuinfektion der Sentinels innerhalb der 10 Tage des
Beobachtungszeitraums gereicht hätte. Bei den mit SC35-delNS1 infizierten Tieren war nur
an Tag 1 nach Infektion in den Pharynxtupfern virale RNA nachweisbar, wobei diese
eventuell noch von der intratrachealen Infektion stammte.
30
Pharynx
25
Kloake
SC35-wt
SC35-delNS1
50-CT
20
20
15
10
10
5
0 **
0
* * * * ** * * *
2
4
6
8
10
Zeit (Tage nach Infektion)
0 **** *
0
2
* * * ** * * *
4
6
8
10
Zeit (Tage nach Infektion)
Abbildung 4.14: Ausscheidung von SC35-wt und SC35 delNS1
Sechs Wochen alte Hühner wurden intratracheal mit 1x106 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe). RNAExpression des viralen NP-Gens in Pharynx- (linke Abbildung) und Kloakentupfern (rechte Abbildung). Die Sterne
markieren Werte, die unter dem Detektionslimit liegen. (CT = cycle of threshold)
Die Anwesenheit von biologisch aktivem IFN in Lunge, Milz und Serum wurde wiederum
mittels Bioassay untersucht (Abbildung 4.15). Auffallend war, dass SC35-wt bereits nach
20 Stunden mehr IFN in den Lungen der infizierten Hühner induzierte als SC35-delNS1.
Nach 66 Stunden war der Unterschied noch größer. Dieses Ergebnis steht in starkem
Gegensatz zu den Ergebnissen der vorherigen Experimente in CEFs und in der Maus, bei
E
72
Ergebnisse
denen die delNS1-Mutante stets viel mehr IFN induzierte. Eine Infektion mit einem aviären
Influenza-A-Stamm, wie SC35-wt, scheint zu einer starken IFN-Antwort zu führen, welche
die Hühner aber nicht vor der Infektion schützt. SC35-delNS1 schien hingegen zu attenuiert
zu sein, um überhaupt eine starke IFN-Antwort zu induzieren, so dass eine geringe Menge an
Hühner-IFN (Units/ml)
IFN schon ausreichte, um das Virus zu inhibieren.
1000
Lunge
SC35-wt
SC35-delNS1
800
600
400
200
0
0
20
66
Zeit (h nach Infektion)
Abbildung 4.15: IFN-Induktion von SC35-wt und SC35-delNS1 in adulten Hühnern
Sechs Wochen alte Hühner wurden intratracheal mit 1x106 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe). An den
angegebenen Zeitpunkten wurde jeweils eine Gruppe Hühner getötet und die IFN-Menge in der Lunge mittels Bioassay
bestimmt. 1 ml Probe entspricht ungefähr 10% an Lungengewebe.
Als letztes wurde noch überprüft, ob es zu einer Serokonversion gekommen ist, also ob die
infizierten Hühner eine Antikörperantwort gegen SC35-wt beziehungsweise SC35-delNS1
entwickelt hatten. Dazu wurde ein ELISA durchgeführt, der auf der Detektion von IgMAntikörpern gegen das virale Nukleoprotein basiert. Abbildung 4.16 zeigt, dass sowohl die
mit SC35-wt als auch die mit SC35-delNS1 infizierten Hühner serokonvertierten. Nach
66 Stunden hatten in beiden Fällen erst einige Hühner Antikörper gebildet, aber zu späteren
Zeitpunkten waren alle Hühner serokonvertiert. Das zeigt sehr deutlich, dass die initiale
Menge an SC35-delNS1 ausreichte, um eine Antikörperantwort zu induzieren, auch wenn das
Virus zu attenuiert war, um sich auszubreiten oder Krankheitssymptome auszulösen.
Weiterhin ist zu erkennen, dass alle Sentinels seronegativ blieben, also keine
Antikörperantwort etabliert hatten. Zusammen mit den qPCR-Ergebnissen zeigt dies, dass die
mit SC35-wt infizierten Hühner in der Tat nicht genug Virus ausgeschieden hatten, um
selbiges zu übertragen.
E
73
negativ
Ergebnisse
60
50
40
positiv
Reaktivität (%)
70
30
20
SC35-delNS1, d10
SC35-delNS1, 66h
Sentinels
SC35, d4-d6
SC35, 66h
10
Abbildung 4.16: Serologische Untersuchung SC35-wt- und SC35-delNS1-infizierter Hühner
Sechs Wochen alte Hühner wurden intratracheal mit 1x106 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe). An den
angegebenen Zeitpunkten wurde je einer Gruppe Blut abgenommen und das Vorhandensein von IgM-Antikörpern gegen NP
mittels ELISA untersucht. Die unterschiedlichen Symbole innerhalb einer Gruppe repräsentieren verschiedene Hühner.
SC35-wt-infizierte Hühner wurden zwischen Tag 4 und 6 euthanasiert, SC35-delNS1-infizierte Hühner an Tag 10.
4.1.6 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten SC35-Viren in adulten Hühnern zu früheren Zeitpunkten
Eine Möglichkeit, warum nach Infektion mit SC35-delNS1 kein IFN messbar war, ist, dass
dieses Virus zu sehr früheren Zeitpunkten eine große Menge an IFN induziert und dadurch
sofort in der Ausbreitung inhibiert wird. Darum wurden erneut adulte Hühner mit SC35-wt
und SC35-delNS1 Viren infiziert. Dieses Mal wurde zusätzlich noch die SC35-NS1(126)Mutante verwendet. Aufgrund der effizienteren Replikation von SC35-NS1(126) im
Vergleich zu SC35-delNS1 in den TOCs (Abbildung 4.9) sollte diese Mutante einen
intermediären Phänotyp aufweisen und eventuell mehr Aufschlüsse darüber geben, wie sich
die IFN-Antwort im Huhn nach Influenza-A-Virusinfektion verhält. Von infizierten Hühnern
wurden wiederum Lunge, Milz und Blut entnommen und auf Anwesenheit von Virus und IFN
getestet. Dieses Mal wurden die Proben jedoch schon nach 8 und 16 Stunden entnommen.
Abbildung 4.17 zeigt, dass zu diesen frühen Zeitpunkten die Menge an viraler RNA aller drei
Viren in der Lunge vergleichbar war, ähnlich wie nach 20 Stunden im ersten Versuch
(Abbildung 4.13).
E
74
50-CT
30
Ergebnisse
Lunge
SC35-wt
SC35-NS1(126)
SC35-delNS1
20
10
0
**0 *
8
16
Zeit (h nach Infektion)
Abbildung 4.17: Wachstumsverhalten von SC35-wt und den SC35-Mutanten in adulten Hühnern
Drei Wochen alte Hühner wurden intratracheal mit 1x106 ffu/Tier der angegebenen Viren infiziert (n=6/Gruppe). Der
Zustand der Hühner wurde täglich überprüft. RNA-Expression des viralen NP-Gens in der Lunge wurde an den angegebenen
Zeitpunkten bestimmt. Die Sterne markieren Werte, die unter dem Detektionslimit liegen. (CT = cycle of threshold)
Die eigentlich wichtige Frage betraf aber die IFN-Induktion. Deshalb wurde Lungen-, Milz-,
und Plasmaproben auf biologisch aktives IFN untersucht (Abbildung 4.18). Die delNS1Mutante induzierte jedoch zu keinem Zeitpunkt mehr IFN als SC35-wt. Auch SC35-NS1(126)
induzierte nicht mehr IFN in der Lunge. Wie erwartet wurde in der Milz kaum IFN gemessen.
Die Analyse des Plasmas ergab das gleiche Ergebnis. Insgesamt konnte daraus
geschlussfolgert werden, dass SC35-delNS1 und SC35-NS1(126) keine großen Mengen an
IFN im Huhn induzieren, im Gegensatz zu SC35-wt, das zu späteren Zeitpunkten nach
3
2
1
0
***
0
8
16
Zeit (h nach Infektion)
4
Milz
Hühner-IFN
(Units/ml Plasma)
Lunge
4
Hühner-IFN
[log10 (Units/g Organ)]
Hühner-IFN
[log10 (Units/g Organ)]
Infektion eine deutlich größere Menge an Typ I IFN induzierte.
3
2
1
0
0
8
16
Zeit (h nach Infektion)
1.5
Plasma
SC35-wt
SC35-NS1(126)
SC35-delNS1
1.0
0.5
0.0
***
0
**
8
16
Zeit (h nach Infektion)
Abbildung 4.18: IFN-Induktion von SC35-wt und den SC35-Mutanten in adulten Hühnern
Drei Wochen alte Hühner wurden intratracheal mit 1x106 ffu/Tier der angegebenen Viren infiziert (n=6/Gruppe). An den
angegebenen Zeitpunkten wurde jeweils eine Gruppe Hühner getötet und die IFN-Menge in der Lunge (linke Abbildung), in
der Milz (mittlere Abbildung) und im Plasma (rechte Abbildung) mittels Bioassay bestimmt. Die Sterne markieren Werte, die
unter dem Detektionslimit liegen.
4.1.7 Interferon-Sensitivität der rekombinanten SC35-Viren in Hühnerzellen
Aufgrund der unerwarteten Ergebnisse der in vivo-Versuche im Huhn wurde die IFNSensitivität der Viren in Hühnerzellen getestet. Eine mögliche Erklärung dafür, dass SC35-wt
eine große Menge an IFN im Huhn induzierte und trotzdem in der Lage war, sich
auszubreiten und Krankheit zu induzieren, ist ein großes Maß an IFN-Resistenz des wt-Virus.
E
75
Ergebnisse
Deshalb wurden zuerst Hühnerzellen für 24 Stunden mit Hühner-IFN-α vorbehandelt und
anschließend mit SC35-wt und den Mutanten infiziert. Nach der Infektion wurden die Zellen
wiederum mit IFN-haltigem Medium inkubiert. Alle 12 Stunden wurde ein Aliquot
abgenommen und titriert. Da das Hühner-IFN-α keine Wirkung auf canine MDCK-NS1-GFPZellen hat, brauchte es nicht inaktiviert zu werden. Die größte Auswirkung auf das
Viruswachstum hatte das Hühner-IFN im Fall von SC35-delNS1 (Abbildung 4.19). Schon bei
100 U/ml IFN war kaum Virus im Überstand nachweisbar. SC35-wt wurde hingegen auch
von 1000 U/ml kaum inhibiert und zeigte nur eine leichte Verzögerung im Wachstum. Nach
60 Stunden erreichte es vergleichbar hohe Titer wie ohne IFN-Vorbehandlung. Bei den Cterminal verkürzten NS1-Mutanten reduzierte sich der Titer nach Behandlung mit 1000 U/ml
um den Faktor 100 auf ca. 1x104 - 1x105 ffu/ml. Insgesamt zeigte sich also, dass SC35-wt
erstaunlich resistent gegenüber der Wirkung von Hühner-IFN-α war. Im Gegensatz dazu
reagierte SC35-delNS1 sehr sensitiv auf IFN-α. Die C-terminal verkürzten NS1-Mutanten
zeigten alle einen intermediären Phänotyp, was sich darin äußerte, dass die Titer bei hohen
IFN-Mengen zu allen Zeitpunkten reduziert waren.
SC35-wt
Virustiter
[log10 (ffu/ml)]
8
6
6
4
4
2
2
0
0
12
24
SC35-delNS1
8
36
48
60
0 U/ml
100 U/ml
1000 U/ml
0
0
Zeit (h nach Infektion)
Virustiter
[log10 (ffu/ml)]
8
SC35-NS1(73)
8
12
24
36
SC35-NS1(99)
8
6
6
6
4
4
4
2
2
2
0
12
24
36
48
Zeit (h nach Infektion)
60
60
SC35-NS1(126)
0 U/ml
100 U/ml
1000 U/ml
0
0
0
48
Zeit (h nach Infektion)
0
12
24
36
48
Zeit (h nach Infektion)
60
0
12
24
36
48
60
Zeit (h nach Infektion)
Abbildung 4.19: IFN-Sensitivität von SC35-wt und den SC35-Mutanten in Hühnerzellen
Semi-konfluente CEFs wurden in Medium gehalten, das 24 Stunden vor der Infektion mit SC35-wt (linke, obere Abbildung),
SC35-delNS1 (rechte, obere Abbildung), SC35-NS1(73) (rechte, untere Abbildung), SC35-NS1(99) (mittlere, untere
Abbildung) beziehungsweise SC35-NS1(126) (rechte, untere Abbildung) mit den angegebenen Konzentrationen an HühnerIFN-α versetzt wurde. Für die Infektion wurde eine geringe Virusdosis verwendet (MOI 0,001). Nach der Infektion wurden
die Zellen wiederum mit IFN-haltigem Medium inkubiert. Die Virustiter im Zellkulturüberstand wurden an den angegebenen
Zeitpunkten bestimmt. Das Ergebnis von drei unabhängigen Experimenten ist dargestellt.
E
76
Ergebnisse
4.1.9 Interferon-Sensitivität von SC35-wt und SC35-NS1(126) in Trachealorgankulturen
Um die Hypothese zu bestätigen, dass SC35-wt im Huhn trotz großer IFN-Mengen so gut
replizieren konnte weil es einen hohen Grad an IFN-Resistenz aufwies, wurden auch TOCs
mit Hühner-IFN-α vorbehandelt und anschließend mit SC35-wt und SC35-NS1(126) infiziert.
Da SC35-delNS1 überhaupt nicht in der Lage war, in diesen Kulturen zu replizieren, wurde es
in diesem Experiment nicht eingesetzt. Die Trachealringe wurden für 8 Stunden mit
1000 Unit Hühner-IFN-α vorbehandelt, was laut Abbildung 4.8 ausreicht, um eine Induktion
der ISGs zu erzielen. Anschließend wurden die TOCs mit den beiden Viren infiziert.
Wiederum wurden die Kulturen nach 1 Stunde Infektion gewaschen und mit IFN-haltigem
Medium inkubiert. Das Ergebnis ist in Abbildung 4.20 dargestellt. Bei den SC35-NS1(126)infizierten Kulturen konnte kein Virus mehr nachgewiesen werden. SC35-wt konnte trotz der
großen Menge an Hühner-IFN-α in der Mehrzahl der Kulturen noch replizieren, auch wenn in
diesen der Titer niedriger war. Dies zeigt, dass SC35-wt auch in diesem System ein gewisses
Maß an IFN-Resistenz aufwies und könnte erklären, warum das wt-Virus in der Lage war,
sich in seinem eigentlichen Wirt, dem Huhn, effizient zu vermehren.
SC35-wt
ohne IFN
8
6
6
4
4
2
2
0
0
12
24
36
48
60
Zeit (h nach Infektion)
0
1000U/ml IFN
3
Virustiter
[log10 (ffu/ml)]
Virustiter
[log10 (ffu/ml)]
8
SC35-NS1(126)
0
12
24
36
48
60
Zeit (h nach Infektion)
ohne IFN
3
2
2
1
1
0
0
12
24
36
48
60
0
Zeit (h nach Infektion)
1000U/ml IFN
0
12
24
36
48
60
Zeit (h nach Infektion)
Abbildung 4.20: IFN-Sensitivität von SC35-wt und SC35-NS1(126) in Trachealorgankulturen
TOCs wurden entweder in normalem Medium oder in Medium mit 1000 Unit Hühner-IFN-α gehalten. 8 Stunden nach IFNZugabe wurden die Kulturen mit 100ffu/Ring SC35-wt beziehungsweise SC35-NS1(126) infiziert. Die Virustiter im
Zellkulturüberstand wurden an den angegebenen Zeitpunkten bestimmt. Jeder Punkt stellt einen individuellen Ring dar.
Insgesamt konnte aus den bisherigen Daten geschlossen werden, dass SC35 kein hoch
pathogenes Virus ist und dass dieses Virus daher nicht optimal geeignet ist, um zu
untersuchen, wie sich ein hoch pathogenes aviäres Influenzavirus im Huhn verhält und wie
das Immunsystem des Huhns auf das Virus reagiert.
E
77
Ergebnisse
4.2 Wachstumsverhalten und Interferon-Induktion von R65-wt (H5N1) und
Mutanten in Zellkultur und verschiedenen in vivo-Systemen
Für die weiteren Versuche wurde ein HPAIV vom Stamm H5N1 verwendet, das auf der Insel
Rügen aus einem Schwan isoliert und von dem schon im Vorfeld gezeigt wurde, dass es hoch
pathogen für Hühner ist (252). Dieser H5N1-Stamm, A/cygnus cygnus/RuegenGermany/R65/2006, wird im Folgenden als R65 bezeichnet. Aufgrund der höheren Virulenz
war die Wahrscheinlichkeit größer, dass die Viren besser und schneller replizieren und
infolgedessen auch die Mutanten noch in der Lage sind zu replizieren, so dass ein deutlicheres
Bild des Zusammenspiels mit dem angeborenen Immunsystem des Huhns zu erkennen sein
sollte als mit SC35.
Die bidirektionalen Plasmide für den Rescue der rekombinanten R65-Viren wurden wiederum
von Kooperationspartnern der Insel Riems zur Verfügung gestellt (Abbildung 4.21).
wt NS-Gen
875nt
wt-NS1 mRNA
225aa
NEP mRNA
121aa
AS 10
AAA
AAA
AS 162
delNS1-Gen
418nt
delNS1-mRNA
10aa
NEP mRNA
121aa
AS 126 AS 162
AAA
AAA
NS1 1-126-Gen
764nt
NS1 1-126-mRNA
126aa
NEP mRNA
121aa
AAA
AAA
Abbildung 4.21: Verwendete NS1-Konstrukte für den Rescue der R65-Viren
AS = Aminosäure; nt = Nukleotid
Der Rescue von R65-delNS1 auf MDCK-NS1-GFP/293T-Kokultur war genauso effizient wie
der R65-wt-Rescue (Tabelle 4.2). Allerdings schlugen alle Versuche, C-terminal verkürzte
Mutanten zu generieren fehl. Die Sequenzierung der verwendeten Plasmide zeigte, dass keine
Mutationen aufgetreten waren, die den Fehlschlag erklären könnten. Auch eine erneute
Klonierung der Segmente in einen anderen Vektor brachte keine Verbesserung. Außerdem
konnte ausgeschlossen werden, dass NS1(126) von R65 aufgrund von toxischen Sequenzen
nicht exprimiert werden konnte (siehe Abbildung 4.41). Um virusstammspezifische Gründe
auszuschließen, wurde in einem 7+1-Ansatz versucht, SC35-Mutanten zu generieren, die das
NS1(126) von R65 besaßen. Dafür wurde ein Plasmid, welches das 8. Segment von R65
enthielt und 7 Plasmide für die übrigen Segmente von SC35 verwendet. Auch dieser Versuch
misslang. Es wurde schon für verschiedenste Influenza-A-Stämme beschrieben, dass C-
E
78
Ergebnisse
terminal verkürzte NS1-Mutanten generiert werden können (187, 221, 247). Allerdings ist das
NS1-Protein von R65 um 5 Aminosäuren kürzer als das NS1 vieler anderer Stämme, wie
SC35. Durch die Deletion an Aminosäureposition 80-84 ist die Aminosäuresequenz am
direkten C-Terminus des NS1-Proteins eine andere. Deshalb ist eine mögliche Erklärung, dass
durch das Vorhandensein anderer Aminosäuren am direkten C-Terminus des NS1-Proteins,
eventuell nicht charakterisierte Sequenzmotive entfernt wurden. Allerdings gilt das nur für die
Mutanten mit dem NS1(1-126) und NS1(1-99), nicht aber für die Mutante mit dem NS1(173). Um aber dennoch R65-Mutanten mit einem C-terminal-verkürzten NS1-Protein zu
generieren, wurde in einem weiteren 7+1-Ansatz eine Mutante generiert, die 7 Segmente von
R65 besaß und das 8. Segment von SC35. Die Generierung dieser Mutante, die der
Einfachheit halber R65-trunkNS1 genannt wird, war erfolgreich. Um den Einfluss der
veränderten NS1-Sequenz von SC35 im Vergleich zu R65 zu testen, wurde zusätzlich ein
weiteres Virus generiert, welches das Volllängen-NS1-Protein von SC35 besaß [R65NS1(SC35)]. Die korrekte Sequenz des 8. Segmentes wurde wie auch schon bei den SC35Viren durch Sequenzanalysen bestätigt.
Bezeichnung
Merkmal
Rescue
R65-wt
8 Segmente von R65
+
R65-NS1(73)
7 Segmente von R65, 8. Segment besitzt NS1-Protein mit 73 Nterminalen Aminosäuren + NEP-Protein von R65
-
R65-NS1(99)
7 Segmente von R65, 8. Segment besitzt NS1-Protein mit 99 Nterminalen Aminosäuren + NEP-Protein von R65
-
R65-NS1(126)
7 Segmente von R65, 8. Segment besitzt NS1-Protein mit 126 Nterminalen Aminosäuren + NEP-Protein von R65
-
R65-trunkNS1
7 Segmente von R65, 8. Segment besitzt NS1-Protein mit 126 Nterminalen Aminosäuren + NEP-Protein von SC35
+
R65-NS1(SC35) 7 Segmente von R65, 8. Segment von SC35
+
R65-delNS1
+
7 Segmente von R65, besitzt kein NS1-Protein, aber NEP-Protein
von R65
Tabelle 4.2: Tabelle der generierten rekombinanten R65-Viren
4.2.1 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten R65-Viren in Hühnerzellen
Zunächst wurde das Wachstum der R65-Viren in aviären Zellen untersucht. Dazu wurden
CEFs mit einer geringen MOI infiziert. Wie in Abbildung 4.22 gezeigt ist, waren alle drei
Viren in der Lage, in diesen Zellen zu replizieren. Wie erwartet war R65-wt in der Lage, zu
E
79
Ergebnisse
hohen Titern von ungefähr 108 ffu/ml zu wachsen. Aber auch R65-trunkNS1 zeigte ein gutes
Wachstum, wie anhand der Titer von ca. 106 ffu/ml ersichtlich ist. R65-delNS1 war stärker
Virustiter
[log10 (ffu/ml)]
attenuiert und replizierte zu Titern um 104-105 ffu/ml.
8
6
4
R65-wt
R65-trunkNS1
R65-delNS1
2
0
0
12
24
36
48
60
Zeit (h nach Infektion)
Abbildung 4.22: Wachstumsverhalten von R65-wt und den R65-Mutanten in Hühnerzellen
Semi-konfluente CEFs wurden mit R65-wt (gefüllte Kreise), R65-trunkNS1 (Diamanten) beziehungsweise R65-delNS1
(gefüllte Dreiecke) mit einer MOI von 0,001 infiziert. Die Virustiter im Zellkulturüberstand wurden an den angegebenen
Zeitpunkten bestimmt. Das Ergebnis von drei unabhängigen Experimenten ist dargestellt.
Um herauszufinden, ob die Unterschiede in der Replikation auf eine unterschiedliche IFNInduktion beziehungsweise -Inhibition zurückzuführen sind, wurde zuerst eine semiquantitative RT-PCR durchgeführt. Dazu wurden CEFs mit einer MOI von 0,5 der jeweiligen
Viren infiziert und 10 Stunden nach Infektion wurde die RNA für die RT-PCR isoliert.
Abbildung 4.23 zeigt einen deutlichen Anstieg der Transkription des IFN-β-Gens in Zellen,
die mit R65-delNS1 infiziert waren, im Vergleich zu R65-wt- und R65-trunkNS1-infizierten
S1
R6
5 -d
elN
S1
mo
ck
ru
nk
N
R6
5-t
R6
5 -w
t
Zellen. Die Level der NP-, NS1- und Aktin-RNA waren vergleichbar.
IFNβ
R65-NS1
R65-NP
β-Aktin
Abbildung 4.23: IFN-Induktion von R65-wt und den R65-Mutanten in Hühnerzellen
Konfluente CEFs wurden mit den verschiedenen Viren mit einer MOI von 0,5 infiziert und 10 Stunden nach Infektion wurde
die IFN-Induktion mittels RT-PCR bestimmt. Ein repräsentatives Ergebnis ist dargestellt.
E
80
Ergebnisse
Für die Messung von biologisch aktivem IFN im Überstand wurde auch in diesem Fall zuerst
getestet, ob die CEC-32#511-Reporterzellen des Bioassays nach Infektion mit R65-wt oder
R65-delNS1 IFN produzieren. Abbildung 4.24 zeigt aber, dass auch mit dem aggressiveren
H5N1-Virus keine direkte Mx-Induktion erfolgte, was bedeutete, dass die Viren für die
Hühner-IFN (Units/ml)
Durchführung des Bioassays nicht inaktiviert werden mussten.
4
R65-wt
4
3
3
2
2
1
1
0
106 105 104 103 102 10
1 10-1 10-2 10-3 10-4 10-5 10-6 mock
0
R65-delNS1
106 105 10 4 10 3 10 2 10
1 10-1 10-2 10-3 10-4 10 -5 10 -6 mock
ffu
ffu
Abbildung 4.24: Test der CEC-32#511-Zellen auf IFN-Induktion nach Infektion mit R65-wt und R65-delNS1
CEC-32-Zellen, die stabil mit einem Plasmid (#511), welches das Luziferasegen unter Kontrolle des Hühner-Mx-Promotors
trägt, transfiziert waren, wurden für 1 Stunde mit den angegebenen Virusdosen von R65-wt (linke Abbildung) und R65delNS1 (rechte Abbildung) infiziert. Nach 6-stündiger Inkubation mit Medium wurden die Zellen lysiert und die LuziferaseAktivität wurde bestimmt. Anhand eines IFN-Standards wurde die Luziferase-Aktivität in IFN-Units umgerechnet.
Deshalb wurde IFN in den Überständen infizierter CEFs mittels Bioassay gemessen
(Abbildung 4.25). Wiederum war R65-wt in der Lage, die IFN-Produktion zu inhibieren,
wohingegen R65-delNS1 die Expression großer Mengen an IFN induzierte. R65-trunkNS1
war, wie aufgrund der C-terminalen Deletion anzunehmen war ein weniger guter IFN-
150
100
m
oc
k
un
kN
R
65
-tr
R6
5w
el
N
S1
*
R6
5d
0
S1
50
t
Hühner-IFN (Units/ml)
Induktor als R65-delNS1, induzierte jedoch deutlich mehr IFN als R65-wt.
Abbildung 4.25: IFN-Induktion von R65-wt und den R65-Mutanten in Hühnerzellen
Konfluente CEFs wurden mit einer MOI von 0,5 infiziert und nach 24 Stunden mittels Bioassay auf IFN-Aktivität im
Überstand untersucht. Der Stern markiert Werte, die unter dem Detektionslimit liegen. Das Ergebnis von drei unabhängigen
Experimenten ist dargestellt.
E
81
Ergebnisse
4.2.2 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten R65-Viren in Trachealorgankulturen
Als nächstes wurden wiederum TOCs infiziert und getestet, wie gut R65-wt und die Mutanten
in diesen Ringen replizieren konnten (Abbildung 4.26). Erneut war R65-wt in der Lage, zu
hohen Titern von ca. 106 ffu/ml zu wachsen, aber auch R65-trunkNS1 replizierte relativ gut
nach Infektion mit einer geringen Virus-Dosis. Nach Infektion mit R65-delNS1 konnte
unabhängig von der Menge mit der infiziert wurde in keinem Fall Wachstum festgestellt
werden. Auch diese Virusmutante scheint zu stark attenuiert zu sein, als dass sie in diesem ex
Virustiter
[log10 (ffu/ml)]
vivo-System wachsen könnte.
7
6
5
4
3
2
1
0
R65-wt
0
12
24
36
48
60
Zeit (h nach Infektion)
7
6
5
4
3
2
1
0
R65-trunkNS1
0
12
24
36
48
60
Zeit (h nach Infektion)
7
6
5
4
3
2
1
0
R65-delNS1
0
12
24
36
48
60
Zeit (h nach Infektion)
Abbildung 4.26: Wachstumsverhalten von R65-wt und den R65-Mutanten in Trachealorgankulturen
TOCs wurden mit 100 ffu/Ring von R65-wt (linke Abbildung), R65-trunkNS1 (mittlere Abbildung) beziehungsweise R65delNS1 (rechte Abbildung) infiziert. Die Virustiter im Zellkulturüberstand wurden an den angegebenen Zeitpunkten
bestimmt. Jeder Punkt stellt einen individuellen Ring dar.
Um auch hier den Einfluss der IFN-Induktion beziehungsweise –Inhibierung auf das
Viruswachstum zu bestimmen, wurden TOCs mit den verschiedenen Viren infiziert und nach
24 Stunden wurde mittels Bioassay die IFN-Produktion evaluiert. Wie in Abbildung 4.27
deutlich zu erkennen ist, induzierte R65-wt geringe Mengen an IFN, während R65-trunkNS1
viel IFN induzierte. Auch in den mit R65-delNS1 infizierten TOCs war nur eine geringe
Menge an IFN zu messen. Wahrscheinlich war die vom delNS1-Virus induzierte Menge an
IFN ausreichend, um die Replikation vollständig zu inhibieren, wie es auch bei SC35 der Fall
war. Diese Ergebnisse zeigen, dass R65-wt in der Lage war, die IFN-Produktion zu
inhibieren, im Gegensatz zu den Mutanten, die große Mengen an IFN induzieren. Diese Daten
bestätigten die Ansicht, dass das NS1-Protein unabdingbar für die Inhibierung der IFN-α/βvermittelten Immunantwort in Zellkultur, aber auch in einem aviärem ex vivo-System ist.
E
Ergebnisse
2000
1500
1000
500
m
oc
k
0
R
65
-w
R
65
t
-tr
un
kN
S1
R
65
-d
el
N
S1
Hühner-IFN (Units/ml)
82
Abbildung 4.27: IFN-Induktion von R65-wt und den R65-Mutanten in Trachealorgankulturen
TOCs wurden mit 104 ffu/Ring der angegebenen Viren infiziert und nach 24 Stunden mittels eines Bioassays auf IFNAktivität im Überstand untersucht. Jeder Punkt stellt einen individuellen Ring dar
4.2.3 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten R65-Viren in Mx-positiven Mäusen
Die Infektionsstudien mit den SC35-Viren im Huhn und die Resultate beider Virusstämme
(R65 und SC35) in TOCs lieferten unerwartete Ergebnisse. Die delNS1-Mutanten induzierten
im Gegensatz zu den wt-Viren keine großen Mengen an IFN. Allerdings waren sie auch nicht
in der Lage, zu detektierbaren Titern zu wachsen, was nahe legt, dass eine geringe IFNMenge ausreicht, um das Wachstum dieser Viren zu inhibieren. Um zu untersuchen, ob diese
Tatsache eine Besonderheit des aviären Systems ist, und ob es fundamentale Unterschiede
zwischen dem verwendeten aviären R65-Influenza-Stamm und Standard-Laborstämmen in
Bezug auf die IFN-Induktion in Lungengeweben von Mäusen gibt, wurden Mx-positive
Mäuse intranasal mit einer nicht letalen Dosis infiziert. Da für H5N1-Stämme gezeigt wurde,
dass sie ohne vorherige Adaptation in Mäusen replizieren können (57, 141), mussten die R65Viren nicht zuvor an die Maus adaptiert werden. 24 Stunden nach der Infektion wurden die
Lungen entnommen und die Virustiter bestimmt. In Abbildung 4.28 ist sehr deutlich zu
erkennen, dass R65-wt ohne vorherige Adaptation in den Mäusen replizieren konnte. Die
LD50 (lethal dose 50) in diesen Mx-positiven Mäusen lag bei 2x105 ffu. Auch R65-trunkNS1
wuchs zu Titern von 103 ffu/Lunge und war damit stark attenuiert. Die LD50 dieses Virus
wurde nicht genau bestimmt. Allerdings kann festgestellt werden, dass sie höher war als die
von R65-wt. Nur R65-delNS1 war überhaupt nicht in der Lage, in den Mäusen zu replizieren.
E
Ergebnisse
5
4
3
2
1
*
R
un
kN
R
65
-tr
R
65
-d
e
S1
lN
S1
0
65
-w
t
Virustiter
[log10 (ffu/ Lunge)]
83
Abbildung 4.28: Wachstumsverhalten von R65-wt und den R65-Mutanten in den Lungen B6-Mx1-positiver Mäuse
B6-Mx1-positive-Mäuse wurden intranasal mit einer nicht-letalen Dosis (5x104 ffu/Maus) der angegebenen Viren infiziert
(n=5/Gruppe). 24 Stunden nach Infektion wurden die Lungen der Mäuse entnommen und die Virustiter im Gewebe bestimmt.
Der Stern markiert Werte, die unter dem Detektionslimit liegen.
Auch hier wurde wiederum überprüft, ob die Fähigkeit, die IFN-Antwort zu inhibieren und
die Replikationsfähigkeit der Viren korrelierten. Dazu wurden erneut Mäuse infiziert und die
IFN-Antwort in der Lunge nach 24 Stunden mittels ELISA analysiert (Abbildung 4.29). Die
stärksten Signale wurden in den Lungen delNS1-infizierter Mäuse gefunden. R65-trunkNS1
war ein schwächerer IFN-Induktor, induzierte jedoch noch mehr IFN als R65-wt, das in der
Lage war, die IFN-Produktion fast vollständig zu inhibieren. Diese Ergebnisse spiegeln
vollständig die Ergebnisse der Zellkulturversuche wider. Die Tatsache, dass R65-delNS1
überhaupt nicht detektierbar war, aber hohe Mengen an IFN induzierte, deutete darauf hin,
dass die initiale Replikation oder sogar nur die Infektion der ersten Zellen für die Induktion
einer starken IFN-Antwort ausreichte. Diese Ergebnisse zeigen, dass sich die hoch
pathogenen aviären R65-Viren in Mäusen bezüglich des Wachstums und der Fähigkeit IFN zu
2000
1500
1000
500
R
65
-tr
m
oc
k
0
R
65
-w
t
un
kN
S1
R
65
-d
el
N
S1
Maus-IFN-β
β (pg/ml)
induzieren wie andere Influenza-Laborstämme verhalten.
Abbildung 4.29: IFN-Induktion von R65-wt und den R65-Mutanten in der Lunge B6-Mx1-positiver Mäuse
B6-Mx1-positive Mäuse wurden intranasal mit einer nicht letalen Dosis (5x104 ffu/Maus) der angegebenen Viren infiziert
(n=5/Gruppe). 24 Stunden nach Infektion wurden die Lungen der Mäuse entnommen und die IFN-β-Menge mittels ELISA
bestimmt.
E
84
Ergebnisse
4.2.4 Untersuchung des Wachstumsverhaltens und der Interferon-Induktion der
rekombinanten R65-Viren in adulten Hühnern
Die wichtigste Fragestellung war, wie sich der hoch pathogene R65-Stamm in seinem
natürlichen Wirt, dem Huhn, verhält und ob die verschiedenen Virus-Mutanten in der Lage
sind zu replizieren. Dafür wurden wiederum adulte Hühner intratracheal infiziert und nach
verschiedenen Zeitpunkten Proben für die weitere Analyse entnommen.
Als Kontrolle wurde zusätzlich eine Gruppe Hühner mit R65-NS1(SC35) infiziert, um zu
überprüfen, ob der Austausch des NS1-Proteins einen Einfluss auf die Virulenz hat. Je eine
Gruppe wurde wiederum beobachtet und bei Krankheitsanzeichen wurden die Tiere
geschlachtet. In Abbildung 4.30 sind die Überlebenskurven der jeweiligen Gruppen gezeigt.
Bereits nach 36 Stunden mussten die ersten mit R65-wt infizierten Hühner getötet werden und
keines lebte länger als 48 Stunden. Dieses Virus scheint für Hühner tatsächlich sehr pathogen
zu sein. Die Hühner, die mit dem Kontrollvirus R65-NS1(SC35) infiziert wurden, starben
12 Stunden später. Daraus konnte geschlussfolgert werden, dass durch den Austausch des
8. Segments die Virulenz nur sehr leicht beeinträchtigt war. Alle Hühner, die mit der Mutante
infiziert wurden, die eine komplette Deletion des NS1-Gens enthielt überlebten. Wie SC35delNS1 war auch R65-delNS1 augenscheinlich in Hühnern sehr stark attenuiert und daher
apathogen. Einen großen Unterschied zeigte die C-terminal verkürzte NS1-Mutante. Vier von
fünf Hühnern starben bis 5 Tage nach Infektion und nur ein Huhn überlebte. Dieser Phänotyp
unterstreicht nochmals die Aggressivität und Virulenz des R65-Stammes im Huhn.
Überleben (%)
100
R65-wt
R65-trunkNS1
R65-delNS1
R65-NS1(SC35)
80
60
40
20
0
0
24
48
72
96
120
Zeit (h nach Infektion)
Abbildung 4.30: Überlebenskurven adulter Hühner infiziert mit R65-wt- und den R65-Mutanten
Fünf Wochen alte Hühner wurden intratracheal mit 6x105 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe). Der
Zustand der Hühner wurde täglich überprüft. Im Falle von starken Krankheitssymptomen wurden die Tiere getötet.
E
85
Ergebnisse
Nach 12, 24 und 72 Stunden wurden Lunge, Milz und Gehirn entnommen und auf
Virusreplikation untersucht (Abbildung 4.31). R65-wt wurde bereits 12 Stunden nach
Infektion sowohl in der Lunge als auch in der Milz detektiert und 24 Stunden nach Infektion
im Gehirn, was zeigt, dass dieses Virus sich sehr schnell systemisch ausbreitete. Auch R65trunkNS1 replizierte in der Lunge zu vergleichbaren Titern wie R65-wt, brauchte aber etwas
länger, um sich auszubreiten. Nur R65-delNS1 war zu keinem Zeitpunkt nachweisbar, was
darauf hindeutet, dass diese Mutante zu attenuiert war, um zu replizieren, wie es auch bei
Virustiter
[log10 (ffu/g Organ)]
SC35-delNS1 der Fall war.
8
Lunge
8
Milz
8
6
6
6
4
4
4
2
2
2
0
12
*
24
*
72
*
Zeit (h nach Infektion)
0
**
12
**
24
*
72
Zeit (h nach Infektion)
0
Gehirn
R65-wt
R65-trunkNS1
R65-delNS1
*12
**
**
24
72
*
Zeit (h nach Infektion)
Abbildung 4.31: Wachstumsverhalten von R65-wt und den R65-Mutanten in adulten Hühnern
Fünf Wochen alte Hühner wurden intratracheal mit 6x105 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe). Virustiter
in der Lunge (linke Abbildung), Milz (mittlere Abbildung) und im Gehirn (rechte Abbildung) wurden an den angegebenen
Zeitpunkten bestimmt. Die Sterne markieren Werte, die unter dem Detektionslimit liegen.
Um zu überprüfen, ob R65-delNS1 überhaupt die Lunge der infizierten Hühner erreicht hatte,
wurde eine immunhistologische Analyse auf Lungenschnitten durchgeführt, bei der auf
virales Antigen gefärbt wurde. In Abbildung 4.32 ist anhand der Braunfärbung sehr deutlich
zu erkennen, dass nach 12 Stunden R65-delNS1-infizierte Zellen zu finden waren. Allerdings
wurde diese Mutante bereits nach 30 Stunden vollständig vom Immunsystem eliminiert und
es waren keine infizierten Zellen mehr detektierbar. Im Gegensatz dazu war in den Lungen
R65-wt-infizierter Tiere bereits nach 12 Stunden eine große Anzahl an Zellen infiziert. Nach
30 Stunden hatte sich R65-wt über die gesamte Lunge ausgebreitet.
E
86
Ergebnisse
12 hpi
30 hpi
R65-delNS1
R65-wt
Abbildung 4.32: Ausbreitung von R65-wt und R65-delNS1 in der Lunge adulter Hühner
Fünf Wochen alte Hühner wurden intratracheal mit 6x105 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe).
Histologische Analyse von Lungenschnitten R65-delNS1- (oberer Teil: Vergrößerung 100x beziehungsweise 200x)
beziehungsweise R65-wt-infizierter Hühner (unterer Teil: Vergrößerung 200x beziehungsweise 100x) 12 und 30 Stunden
nach Infektion. Die Pfeile markieren exemplarisch spezifische Braunfärbung des viralen Antigens.
Nach Analyse dieser Daten war die essentielle Frage, wie der IFN-Gehalt in den
entnommenen Organen und im Plasma war, um zu überprüfen, ob das wt-Virus mehr IFN
induziert als die C-terminal verkürzten NS1-Mutanten (Abbildung 4.33). Bereits 12 Stunden
nach Infektion war sehr viel IFN in der Lunge von R65-wt-infizierten Tieren detektierbar.
Aber auch in der Milz und im Plasma war eine große Menge IFN messbar. Auch R65trunkNS1 induzierte sehr viel IFN, allerdings weniger als R65-wt. Außerdem schien die IFNInduktion etwas verzögert zu sein, vor allem in der Milz und im Plasma. Dies könnte damit
zusammenhängen,
dass
diese
Mutante
langsamer
replizierte,
wie
anhand
der
Überlebenskurven und der Titer zu erkennen ist. Allerdings war auch nach 72 Stunden die
induzierte IFN-Menge nicht höher als bei R65-wt-infizierten Hühnern kurz vor deren
Ableben. Die IFN-Menge in den Lungen R65-delNS1-infizierter Hühner war deutlich
geringer. In der Milz war überhaupt kein Anstieg im Vergleich zu den Kontrolltieren zu
erkennen und auch im Plasma war nur sehr wenig IFN detektierbar. Diese Daten zeigen, dass
hoch pathogene Influenza-A-Viren im Huhn die IFN-Produktion nicht inhibieren, wie es in
der Maus der Fall ist, sondern im Gegenteil große Mengen IFN induzieren. Die Mutante mit
E
87
Ergebnisse
der kompletten Deletion des NS1-ORFs war im Hühnersystem zu attenuiert, und daher reichte
Lunge
4
3
2
1
0
0
12
24
72
Zeit (h nach Infektion)
6
Milz
5
4
3
2
1
0
0
12
24
72
Zeit (h nach Infektion)
Hühner-IFN
[log10 (Units/ml Plasma)]
5
Hühner-IFN
[log10 (Units/g Organ)]
Hühner-IFN
[log10 (Units/g Organ)]
wahrscheinlich eine geringe Menge an IFN aus, um die Viren an der Replikation zu hindern.
5
Plasma
R65-wt
R65-trunkNS
R65-delNS1
4
3
2
1
0
0
12
24
72
Zeit (h nach Infektion)
Abbildung 4.33: IFN-Induktion von R65-wt und den R65-Mutanten in adulten Hühnern
Fünf Wochen alte Hühner wurden intratracheal mit 6x105 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe). Zu den
angegebenen Zeitpunkten wurde jeweils eine Gruppe Hühner getötet und die IFN-Menge in der Lunge, (linke Abbildung),
Milz, (mittlere Abbildung) und im Plasma (rechte Abbildung) mittels Bioassay bestimmt.
Die Ergebnisse des Bioassays wurden für R65-wt und R65-delNS1 mittels Northern-Blot
überprüft, da bei diesen beiden Viren der erwartete Unterschied am stärksten war (Abbildung
4.34). Dafür wurden je 10 µg RNA geladen und mit einer radioaktiven, spezifischen Sonde
auf Hühner-IFN-α hybridisiert. Es ist deutlich zu erkennen, dass schon 12 Stunden nach
Infektion IFN-α-RNA in den Lungen R65-wt-infizierter Tiere zu finden war, jedoch keine
IFN-α-RNA in den Lungen delNS1-infizierter Tiere. Dieses Ergebnis stimmte also mit den
Daten des Bioassays überein.
Hühner-IFNα
18S rRNA
Kontrollen
R65-wt
R65-delNS1
R65-wt
12h
R65-delNS1
24h
Abbildung 4.34: IFN-RNA-Induktion von R65-wt und R65-delNS1 in adulten Hühnern
Fünf Wochen alte Hühner wurden intratracheal mit 6x105 ffu/Tier der angegebenen Viren infiziert (n=5/Gruppe). NorthernBlot-Analyse von je 3 Lungen-RNA-Proben von Hühnern infiziert mit R65-wt beziehungsweise R65-delNS1 oder von nicht
infizierten Hühnern als Kontrolle. Der Blot wurde mit einer radioaktiven DNA-Sonde des Hühner-IFNα1-Gens hybridisiert.
Die Ethidiumbromidfärbung der 18S rRNA diente als Ladekontrolle.
Die Ergebnisse der in vivo-Studien mit dem aggressiveren Virus R65 bestätigten also die
SC35-Daten dahingehend, dass hoch pathogene aviäre Influenza-A-Viren im Huhn große
Mengen an IFN induzieren, im Gegensatz zu NS1-Mutanten, die in anderen Systemen
normalerweise eine starke IFN-Antwort hervorrufen.
E
88
Ergebnisse
4.2.5 Interferon-Sensitivität der rekombinanten R65-Viren in Hühnerzellen
Um zu überprüfen, ob die gute Replikationsfähigkeit von R65-wt und R65-trunkNS1 in
Anwesenheit von IFN in den Hühnern auf eine gewisse Resistenz der Viren gegenüber der
Wirkung von IFN hindeutet, wurde wiederum die IFN-Sensitivität untersucht. Als erstes
wurde in Hühnerzellen getestet, wie gut die R65-Varianten nach IFN-Behandlung
replizierten. Dazu wurden die Zellen für 24 Stunden mit IFN vorbehandelt und anschließend
mit einer geringen MOI infiziert. Alle 12 Stunden wurde der Titer gemessen. Abbildung 4.35
zeigt, dass R65-wt sich kaum durch die IFN-Vorbehandlung inhibieren ließ. Nur eine kleine
Verzögerung im Wachstum war nach Behandlung mit 1000 U/ml Hühner-IFN-α zu erkennen.
Nach 60 Stunden erreichte das Virus die gleichen Titer wie in unbehandelten Zellen. Auch
R65-trunkNS1 wies eine erstaunliche IFN-Resistenz auf. Zwischen 12 und 48 Stunden war
nach Behandlung mit 1000 U/ml IFN nur eine Differenz um Faktor 10 zu den unbehandelten
Zellen erkennbar und nach 60 Stunden unterschieden sich die Titer um weniger als Faktor 5.
Nur R65-delNS1 wies wiederum eine sehr starke IFN-Sensitivität auf und war schon bei 100
Virustiter [log10 (ffu/ml)]
U/ml kaum mehr in der Lage zu replizieren.
8
R65-wt
8
R65-trunkNS1
8
6
6
6
4
4
4
2
2
2
0
0
0
12
24
36
48
Zeit (h nach Infektion)
60
0
12
24
36
48
Zeit (h nach Infektion)
60
0
R65-delNS1
0 U/ml
100 U/ml
1000 U/ml
0
12
24
36
48
60
Zeit (h nach Infektion)
Abbildung 4.35: IFN-Sensitivität von R65-wt und den R65-Mutanten in Hühnerzellen
Semi-konfluente CEFs wurden in Medium gehalten, das 24 Stunden vor der Infektion mit R65-wt (linke Abbildung), R65trunkNS1 (mittlere Abbildung) beziehungsweise R65 delNS1 (rechte Abbildung) mit den angegebenen Konzentrationen an
Hühner-IFN-α versetzt worden ist. Für die Infektion wurde eine geringe Virusdosis verwendet (MOI 0,001). Nach der
Infektion wurden die Zellen wiederum mit IFN-haltigem Medium inkubiert.Die Virustiter im Zellkulturüberstand wurden an
den angegebenen Zeitpunkten bestimmt. Das Ergebnis von drei unabhängigen Experimenten ist dargestellt.
4.2.6 Interferon-Sensitivität von R65-wt und R65-trunkNS1 in Trachealorganen
Als nächstes wurde die IFN-Sensitivität der R65-Varianten in TOCs getestet (Abbildung
4.36). R65-wt replizierte nach Infektion mit 100 ffu ohne Hühner-IFN-α-Vorbehandlung zu
Titern von ca. 1x106 ffu/ml. Nach IFN-Vorbehandlung erreichte es die gleichen Titer. Wie
schon in CEFs war eine Verzögerung im Wachstum zu erkennen. Ohne IFN-Vorbehandlung
erreichte R65-wt seinen maximalen Titer schon nach 24-36 Stunden und der Titer nahm
anschließend wieder ab. Nach Vorbehandlung mit 1000 Unit IFN-α wurde der maximale Titer
E
89
Ergebnisse
erst nach 60 Stunden erreicht. Da R65-delNS1 nicht in der Lage war, in den TOCs zu
replizieren, wurde nur noch das Wachstum von R65-trunkNS1 mit und ohne IFNVorbehandlung untersucht. Wie schon in den Hühnerzellen war der IFN-Schutz ineffizient
und die TOCs waren nicht vor einer produktiven Infektion geschützt. Das Wachstum von
R65-trunkNS1 war nur um Faktor 10 niedriger als bei den Kontrollen ohne IFN-Behandlung.
Die Daten zur IFN-Sensitivität in CEFs und TOCs zeigen, dass sowohl R65-wt als auch R65trunkNS1 sehr IFN-resistent waren, wohingegen R65-delNS1 eine hohe IFN-Sensitivität
aufwies.
R65-trunkNS1
7
6
5
4
3
2
1
0
ohne IFN
0
12
24
36
48
60
Zeit (h nach Infektion)
7
6
5
4
3
2
1
0
1000U/ml IFN
Virustiter
[log10 (ffu/ml)]
Virustiter
[log10 (ffu/ml)]
R65-wt
0
12
24
36
48
60
Zeit (h nach Infektion)
7
6
5
4
3
2
1
0
ohne IFN
0
12
24
36
48
60
Zeit (h nach Infektion)
7
6
5
4
3
2
1
0
1000U/ml IFN
0
12
24
36
48
60
Zeit (h nach Infektion)
Abbildung 4.36: IFN-Sensitivität von R65-wt und R65-trunkNS1 in Trachealorgankulturen
TOCs wurden entweder in normalem Medium oder in Medium mit 1000 Unit Hühner-IFN-α gehalten. 8 Stunden nach IFNZugabe wurden die Kulturen mit 100ffu/Ring R65-wt beziehungsweise R65-trunkNS1 infiziert. Die Virustiter im
Zellkulturüberstand wurden an den angegebenen Zeitpunkten bestimmt. Jeder Punkt stellt einen individuellen Ring dar.
4.2.6 Interferon-Sensitivität der rekombinanten R65-Viren in Säugerzellen
Aufgrund der unerwartet hohen Resistenz der R65-Viren gegenüber Hühner-IFN war es von
Interesse, wie sich diese Viren in Säugerzellen nach IFN-Behandlung verhalten. Als
Säugerzellen wurden humane Epithelzellen verwendet, die effizient mit verschiedenen
Influenza-A-Stämmen infiziert werden können (172). In diesem Fall wurden A549-Zellen mit
humanen IFNαB/D (huIFN-α) für 24 Stunden vorbehandelt und nach anschließender
Infektion mit einer geringen MOI von 0,001 wurden alle 12 Stunden Überstände genommen
und diese titriert (Abbildung 4.37). R65-wt zeigte nach Behandlung mit der höchsten Dosis
von 1000 U/ml eine Titer-Reduktion um Faktor 100 und R65-trunkNS1 sogar um Faktor
10000. R65-delNS1 war überhaupt nicht in der Lage, in diesen Zellen zu replizieren, auch
nicht ohne IFN-Vorbehandlung. Diese Daten zeigten sehr deutlich, dass IFN im Säugersystem
einen viel größeren Effekt gegen die verwendeten Viren hat als im aviären System.
E
90
Virustiter
[log10 (ffu/ml)]
8
R65-wt
8
Ergebnisse
R65-trunkNS1
8
6
6
6
4
4
4
2
2
2
0
0
0
12
24
36
48
Zeit (h nach Infektion)
60
R65-delNS1
0 U/ml
100 U/ml
1000 U/ml
0
0
12
24
36
48
Zeit (h nach Infektion)
60
0
20
40
60
Zeit (h nach Infektion)
Abbildung 4.37: IFN-Sensitivität von R65-wt und den R65-Mutanten in Säugerzellen
Semi-konfluente A549-Zellen wurden in Medium gehalten, das 24 Stunden vor der Infektion mit R65-wt (linke Abbildung),
R65-trunkNS1) (mittlere Abbildung) beziehungsweise R65-delNS1 (rechte Abbildung) mit den angegebenen
Konzentrationen an IFNαB/D versetzt worden ist. Für die Infektion wurde ein geringe Virusdosis verwendet (MOI 0,001).
Die Virustiter im Zellkulturüberstand wurden an den angegebenen Zeitpunkten bestimmt. Das Ergebnis von drei
unabhängigen Experimenten ist dargestellt.
4.2.8 Interferon-Sensitivität von R65-wt in Mx-positiven Mäusen
In einem nächsten Schritt wurde die IFN-Sensitivität von R65-wt in vivo untersucht. Als
erstes wurden Mäuse infiziert, um zu bestätigen, dass sich die Viren so verhalten wie in der
Literatur angegeben (10, 241) und wie die Zellkulturveruche mit Säugerzellen andeuten. Dazu
wurden Mx+/+-Mäuse intranasal mit 2x104 Unit huIFN-α beziehungsweise PBS behandelt und
nach 8 Stunden mit einer letalen Dosis R65-wt ebenfalls intranasal infiziert. Es wurde bereits
gezeigt, dass huIFNαB/D speziesübergreifend wirken und in den jeweiligen Zellen die IFNSignalkaskade induzieren kann (82). Die Überlebenskurven sind in Abbildung 4.38 A
dargestellt. Durch die IFN-Vorbehandlung waren alle Mäuse vor der letalen Dosis R65-wt
geschützt, während die PBS-vorbehandelten Mäuse alle starben. Auch die Virustiter
(Abbildung 4.38 B) zeigen deutlich, dass IFN im Maussystem einen schützenden Einfluss hat,
da in der Lunge von IFN-behandelten Mäusen nach 42 Stunden überhaupt kein Virus
detektierbar war. In den Kontroll-Mäusen war R65-wt hingegen in der Lage, bis zu Titern von
ca. 1x104 ffu/Lunge zu wachsen. Diese Daten zeigen wiederum mehr als deutlich, dass IFN
im Säugersystem in der Lage ist, vor einer letalen Influenza-A-Virus-Infektion zu schützen,
wie auch schon die Ergebnisse der IFN-Vorbehandlung in Zellkultur andeuteten.
E
91
B
Überleben (%)
100
R65-wt
R65-wt + IFN
80
60
40
20
0
0
1
2
3
4
5
6
7
8
Virustiter
[log10 (ffu/Lunge)]
A
Ergebnisse
5
4
3
2
1
0
R65-wt
*
R65-wt + IFN
Zeit (h nach Infektion)
Abbildung 4.38: IFN-Sensitivität von R65-wt in Mäusen
BALB-Mx1+/+-Mäuse wurden intranasal mit PBS als Kontrolle (n=5) oder 2x104 Units IFNαB/D (n=6) behandelt. Nach
8 Stunden wurden die Mäuse mit einer letalen Dosis (3x105 ffu/Maus) von R65-wt infiziert. (A) Überlebenskurven und (B)
Virustiter in der Lunge 42 Stunden nach Infektion. Der Stern markiert Werte, die unter dem Detektionslimit liegen.
4.2.9 Interferon-Sensitivität von R65-wt in adulten Hühnern
Um eine endgültige Aussage darüber machen zu können, ob es an der hohen IFN-Resistenz
von R65-wt lag, dass dieses Virus in Anwesenheit einer großen Menge an IFN im Huhn zu
replizieren vermag, wurden Hühner intravenös mit einer hohen Dosis von 4x106 Unit HühnerIFN-α beziehungsweise einem Kontrollprotein behandelt. Um eine natürliche Infektion
nachzuahmen, wurde eine dritte Gruppe okulo-nasal mit einer letalen Dosis (50xLD50)
parentalem R65-wt infiziert und 12 Stunden nach der Infektion wurde diese Gruppe mit den
beiden vorbehandelten Gruppen zusammengesetzt. Auf diese Weise sollte durch die
Aufnahme von ausgeschiedenem Virus eine natürliche Infektion der Tiere stattfinden. Die
IFN- beziehungsweise Kontrollprotein-Behandlung wurde 8 und 2 Stunden vor dem
Zusammensetzten mit der infizierten Gruppe und 12 Stunden nach dem Zusammensetzen
durchgeführt (Abbildung 4.39 A). Um die IFN-Behandlung zu überwachen, wurde jeweils 15
Minuten nach der 2. und 3. Behandlung Blut entnommen und auf den IFN-Gehalt im Plasma
getestet. In Abbildung 4.39 B ist ein starker Anstieg der IFN-Konzentration im Plasma nach
den beiden IFN-Injektionen zu sehen. Dies steht im Gegensatz zum Plasma der
kontrollbehandelten Hühner, was darauf schließen ließ, dass zu dem Zeitpunkt des
Zusammensetzens die Effektormechanismen der IFN-Signalkaskade aktiviert worden sind.
Bereits nach 2 Tagen mussten die ersten experimentell infizierten Hühner euthanasiert
werden. Es ist also anzunehmen, dass sie genug Virus ausgeschieden hatten, um es auf die
vorbehandelten Tiere zu übertragen. Die Überlebenskurven der vorbehandelten Tiere sind in
Abbildung 4.39 C dargestellt. Es gab keine signifikanten Unterschiede zwischen dem
Überleben der IFN-behandelten und der kontrollbehandelten Tiere. Alle Hühner starben
innerhalb der ersten 9 Tage. Daraus kann man schließen, dass systemisch appliziertes IFN in
E
92
Ergebnisse
Hühnern keinen schützenden Effekt gegen hoch pathogene aviäre Influenzaviren aufweist.
Diese Ergebnisse stehen in starkem Gegensatz zu den in vivo-Experimenten mit Mäusen, bei
denen IFN die Mäuse vor einer letalen Infektion mit R65-wt schützen konnte.
A
Zusammensetzen
R65-wt
-12h
-8h
0
-2h
+12h
d 10
Beobachtungszeitraum
HühnerIFN-α
C
100
Überleben (%)
4
3
2
1
60
40
20
In
fe
kt
io
n
0
2
4
6
8
10
Tage nach Infektion
H
üh
ne
rIF
N
12
h
2h
vo
r
na
ch
In
fe
kt
io
n
tro
lle
n
K
ne
rIF
N
Hü
h
IFN
Kontrolle
80
0
0
on
Hühner-IFN
[log10 (Unit/ml Plasma)]
B
Abbildung 4.39: IFN-Sensitivität von R65-wt in adulten Hühnern
(A) Schematische Darstellung der experimentellen Vorgehensweise. Eine Gruppe Hühner (n=8) wurde okulo-nasal mit einer
letalen Dosis (50xLD50) parentalem R65-wt infiziert. Nicht infizierte Hühner wurden mit 4x106 Unit Hühner-IFN-α (IFN)
oder einem Kontrollprotein (Kontrolle) 8 und 2 Stunden vor dem Zusammensetzen mit der infizierten Gruppe und
12 Stunden nach dem Zusammensetzen behandelt. Aller Hühner wurden für 10 Tage beobachtet. (B) 15 Minuten nach der 2.
und 3. Vorbehandlung wurde Blut abgenommen, um im Plasma den IFN-Gehalt mittels Bioassay zu bestimmen. (C)
Überlebenskurven der IFN-behandelten (n=8) und der Kontrollgruppe (n=8).
4.2.10 Einfluss des NS1-Proteins von R65 auf den Interferon-Signalweg
Bisher wurde gezeigt, dass R65-wt in Anwesenheit von Hühner-IFN-α in Hühnerzellen,
TOCs und Hühnern replizieren konnte, wahrscheinlich aufgrund seiner hohen IFN-Resistenz.
Das Gleiche galt bis zu einem gewissen Grad auch für R65-trunkNS1. Im Gegensatz dazu
E
93
Ergebnisse
reagierte R65-delNS1 sehr sensitiv auf die Wirkung von IFN-α und war daher apathogen für
Mäuse und Hühner.
Eine weitere mögliche Erklärung für die Tatsache, dass R65-wt in Anwesenheit großer
Mengen an IFN in Hühnern replizieren konnte, abgesehen von der hohen IFN-Resistenz, ist,
dass das NS1-Protein Einfluss auf die IFN-Signalkaskade hat und nicht nur in der Lage ist,
die IFN-Produktion, sondern auch die Wirkung zu inhibieren. Kürzlich wurde gezeigt, dass
NS1 eines H1N1-PR8- beziehungsweise eines H3N2-Victoria-Stammes die Wirkung von
produziertem IFN durch die Aktivierung von so genannten SOCS-Proteinen (suppressor of
cytokine signaling) inhibieren kann (172). Um diese Hypothese zu testen, wurde ein
Reporterassay durchgeführt, bei dem Wachtelzellen (CEC-32) mit einem Reporterkonstrukt
transfiziert wurden. Eine schematische Darstellung ist in Abbildung 4.40 gezeigt.
IFN
pCAGGS-NS1
(12h nach Transfektion)
pRL-SV40-Ren
Hühner-MxP-FF
IFNAR
NS1
?
4
Hühner-Mx-P
3
Luziferase
Renilla-Luziferase-Aktivität
?
?
(12h nach IFN-Behandlung)
Firefly-Luziferase-Aktivität?
Abbildung 4.40: Schematische Darstellung des Luziferase-Reporter-Assays
CEC-32-Zellen werden mit dem Reporterplasmid, welches das Firefly-Luziferasegen unter Kontrolle des durch IFN
induzierbaren Mx-Promotors enthält und einem Plasmid, welches das Renilla-Luziferasegen unter Kontrolle des
konstitutiven SV40-Promotors enthält transfiziert. Des Weiteren wird ein NS1-Plasmid kotransfiziert. 12 Stunden nach
Transfektion werden die Zellen mit 1000 U/ml Hühner-IFN-α für weitere 12 Stunden behandelt und anschließend wird die
Reportergenexpression gemessen.
Das Reporterkonstrukt trug das Luziferasegen unter Kontrolle des Hühner-Mx-Promotors.
Zusammen mit diesem Reporterkonstrukt wurden Expressionsplasmide transfiziert, die
Volllängen-NS1 beziehungsweise trunkierte Versionen verschiedener NS1-Gene enthielten.
Es wurde das NS1 von R65 aber im Vergleich auch die NS1-Proteine von PR8 (H1N1), bei
dem es sich um einen mausadaptierten Laborstamm handelt, und des 1918-Stammes (H1N1),
der für die verheerende Epidemie von 1918 verantwortlich war. 12 Stunden nach der
Transfektion wurden die Zellen mit 1000 U/ml Hühner-IFN-α behandelt und weitere
12 Stunden später wurden die Zellen lysiert und die Luziferaseaktivität gemessen. Wenn die
E
94
Ergebnisse
Hypothese sich bestätigt, sollte das Volllängenprotein von R65-wt in der Lage sein, die IFNSignalkaskade zu inhibieren. Infolgedessen sollte es keine Aktivierung des Mx-Promotors
geben und die Luziferaseaktivität somit geringer sein als nach Transfektion mit Leervektor als
Kontrolle. Das Ergebnis ist in Abbildung 4.41 gezeigt. Ganz deutlich ist zu erkennen, dass die
IFN-Behandlung zu einem starken Anstieg der Luziferase-Aktivität führte. Sobald aber
zusätzlich das R65-NS1-Expressionsplasmid transfiziert wurde, nahm die Luziferase-Aktiviät
drastisch ab. Das zeigte, dass das NS1-Protein anscheinend in der Lage ist, die IFNEffektorkaskade zu inhibieren. Bei Transfektion des NS1(126) von R65 war die Hemmung
aufgehoben. Das Volllängen-NS1 von 1918 konnte ebenfalls die IFN-Kaskade inhibieren,
wohingegen das Volllängen-NS1-Protein von PR8 dazu nicht in der Lage war, wie es auch
schon in der Literatur beschrieben ist (113). Das war auch bei den C-terminalen verkürzten
NS1-Mutanten von PR8 und dem 1918-Stamm der Fall. Diese Daten zeigen, dass das NS1Protein von HPAIV in der Lage ist, mit dem IFN-Signalweg zu interferieren. Diese Tatsache
trägt wahrscheinlich dazu bei, dass R65-wt in Anwesenheit großer Mengen Hühner-IFN-α
replizieren konnte, da es die Wirkung von IFN und somit die Expression vieler antiviraler
ISGs inhibiert.
CEC-32
x-fache Induktion
100
80
60
40
20
8
7
6
5
4
3
2
1
0
NS1
β-Tubulin
1918-NS1(126)
1918-wt
PR8-NS1(126)
PR8-wt
R65-NS1(126)
R65-wt
Kontrolle
Kontrolle
IFN
Abbildung 4.41: Das NS1-Protein von R65-wt interferiert mit dem IFN-Signalweg
CEC-32-Zellen wurden mit dem Reporterplasmid, welches das Firefly-Luziferasegen unter Kontrolle des durch IFN
induzierbaren Mx-Promotors enthält und einem Plasmid, welches das Renilla-Luziferasegen unter Kontrolle des
konstitutiven SV40-Promotors enthält kotransfiziert. Des Weiteren wurden als Kontrolle ein leerer Vektor oder Plasmide, die
für die jeweiligen NS1-Proteine des Influenzavirusstammes R65 (H5N1), PR8 (H1N1) oder des 1918-Stammes (H1N1)
kodieren transfiziert. 12 Stunden nach Transfektion wurden die Zellen mit 1000 U/ml Hühner-IFN-α für weitere 12 Stunden
behandelt und anschließend wurden die Reportergenexpression gemessen. Das Ergebnis von drei unabhängigen
Experimenten ist dargestellt. Die Lysate der Zellen wurden außerdem noch für die Analyse der NS1- und β-TubulinExpression mittels Western-Blot verwendet.
E
95
Diskussion
5. Diskussion
5.1 Generierung der verwendeten Viren
Ziel dieser Arbeit war es, die frühe Immunantwort im Huhn nach Infektion mit HPAIV zu
untersuchen. In Mäusen konnte gezeigt werden, dass eine frühe Induktion der IFN-α/βSignalkette wesentlich zur Kontrolle der Replikation von Influenzaviren beiträgt (68, 142,
231). Im Unterschied dazu ist bisher noch sehr wenig über die Immunantwort auf aviäre
Influenzaviren in ihrem natürlichen Wirt bekannt.
In der vorliegenden Arbeit wurden zwei verschiedene Stämme pathogener aviärer
Influenzaviren untersucht. Der erste Stamm (A/seal/Mass/1/80) ist als Serotyp H7N7
charakterisiert und wurde als hoch pathogen für Hühner beschrieben (132). Als zweites wurde
ein H5N1-Stamm (A/cygnus cygnus/Ruegen-Germany/R65/2006) verwendet, der aus einem
Schwan isoliert worden ist (252). Der Rescue der wt-Viren (SC35-wt und R65-wt) und der
Virusmutanten, welche eine vollständige Deletion im NS1-Gen aufweisen (SC35-delNS1 und
R65-delNS1) gelang ohne weiteres. Die Generierung der C-terminalen NS1-Mutanten
[NS1(1-73), NS1(1-99) und NS1(1-126)] war jedoch nur im Fall des SC35-Stammes
erfolgreich. Möglicherweise wurden durch die C-terminalen Deletionen im Fall des R65Stammes nicht charakterisierte Sequenzmotive entfernt, die das Spleißen des 8. Segments
regulieren und dadurch die Level des NEP-Proteins verändern. Weiterhin könnten die Cterminal verkürzten NS1-Proteine eventuell noch andere Funktionen ausüben, die zu einer
Hemmung des Wachstums führen. Studien mit einem mausadaptierten Virus zeigten, dass
durch die Mutation nur einer Aminosäure im NS1-Protein die Replikation in der Maus IFNunabhängig inhibiert wurde (persönliche Kommunikation S. Steidle).
Obwohl diese C-terminalen NS1-Mutanten bereits für verschiedene Influenza-A-Stämme
generiert und in verschiedenen Zelllinien getestet wurden (114, 187), müssen die
Konsequenzen der NS1-Trunkierung noch systematisch untersucht werden. Talon et al.
konnten zeigen, dass die Länge des NS1-Proteins mit dem Level der Attenuierung der Viren
korreliert (232). In anderen Studien wurde dieser Effekt jedoch nicht beobachtet (187, 214).
Die Daten der vorliegenden Arbeit bestätigen, dass die C-terminale Mutante des SC35Stammes, deren NS1 126 Aminosäuren besaß von den generierten C-terminal verkürzten
NS1-Mutanten in verschiedenen Systemen am besten replizieren konnte. Allerdings
korrelierte die Menge an induziertem IFN zumindest in Hühnerembryo-Fibroblasten und in
Trachealorgankulturen nicht mit der Länge des NS1-Proteins. Eine weitere Studie zeigte, dass
eine Virusmutante, die ein NS1-Protein mit 86 beziehungsweise 93 Aminosäuren besaß im
E
96
Diskussion
Huhn attenuiert war und nicht übertragen wurde (250). Deshalb wurde entschieden, dass für
die in vivo-Versuche in der Maus und im Huhn nur die Mutanten mit dem NS1(126)
eingesetzt wurden. Für den R65-Stamm wurde aus diesem Grund auch nur diese Mutante
generiert.
5.2 Wachstumsverhalten
In dieser Arbeit wurde gezeigt, dass die aviären Influenza-A-Viren SC35-wt und R65-wt in
allen System sehr gut replizieren konnten. Überraschenderweise konnten auch die Mutanten
mit der vollständigen Deletion im NS1-ORF in CEFs bis zu einem gewissen Grad replizieren.
Vergleichbare
NS1-Deletionsmutanten
eines
equinen
beziehungsweise
eines
mausdadaptierten Influenza-A-Stammes waren hingegen nicht in der Lage, in IFNkompetenten Zellen zu wachsen (114, 187). Die TOCs wurden etabliert, um dem eigentlichen
aviären in vivo-System näher zu kommen und infolgedessen zusätzliche Informationen über
das Verhalten aller generierten Viren im aviären in vivo-System zu bekommen. Schon für
andere Viren wurde in diesem ex vivo-System gezeigt, dass es die Replikation unterstützt (30,
32, 161). In TOCs war bei den delNS1-Mutanten allerdings überhaupt keine Replikation zu
detektieren. Das zeigt, dass sich dieses ex vivo-System anders verhält als die CEFs, die vom
gleichen Organismus stammen. Der Grund für diesen Unterschied ist nicht bekannt. Es könnte
jedoch sein, dass bei der Präparation der TOCs auftretende Verletzungen zu einer
Hochregulierung der Immunantwort führen. Erst kürzlich wurde gezeigt, dass durch die
Verletzung des Gewebes bei der Herstellung der Trachealringe unter anderem IL-6, IL-8 und
IL-10 hoch reguliert werden (189). Diese Aktivierung des Immunsystems könnte dazu führen,
dass die delNS1-Viren sofort nach ihrem Eintritt in die Zellen inhibiert werden. Alle Viren
mit C-terminal verkürzten NS1-Proteinen replizierten in CEFs zu ähnlichen Titern wie die wtViren. Nur in TOCs waren die Unterschiede im Titer größer.
Ein zu den TOCs ähnliches Wachstumsverhalten der Viren wurde auch in Mäusen nach
Infektion mit den Viren des R65-Stammes beobachtet. Die SC35-Viren waren aufgrund der
geringeren Virulenz nicht in der Lage ohne vorherige Adaptation in den Mäusen zu hohen
Titern zu wachsen. Es wurde beschrieben, dass das ursprüngliche Isolat aus dem Seehund,
trotz der Ähnlichkeit aller RNA-Segmente zu aviären Viren bis zu einem gewissen Grad in
Säugern replizieren kann. Das an Hühnerzellen adaptierte SC35 ist allerdings nur für Mäuse
pathogen, denen das Mx1-Gen fehlte (199), von dem gezeigt wurde, dass es Resistenz
gegenüber Influenzaviren vermittelt (69). Selbst nach Adaptationsstudien, bei denen SC35 an
E
97
Diskussion
die Maus adaptiert wurde, was in dem Virusstamm SC35M resultierte, wies das Virus nur in
Mx-negativen Mäusen eine hohe Virulenz auf (114). Deshalb wurde das Wachstumsverhalten
in Mx-positiven Mäusen nur mit den Viren des R65-Stammes überprüft, die eine höhere
Pathogenität aufwiesen. R65-trunkNS1 wuchs zu relativ hohen Titern, obwohl es eine
geringere Virulenz aufwies, was auch an der höheren LD50 zu sehen war. Nur R65-delNS1
war überhaupt nicht in der Lage, in der Mauslunge zu detektierbaren Titern zu wachsen.
Die Infektion von adulten Hühnern mit den wt-Viren zeigte, dass beide Viren bereits
12 Stunden nach Infektion in der Lunge replizierten und sich von dort sehr schnell
ausgebreitet hatten. Die spätere Infektion von anderen Organen wie Milz und Gehirn wies auf
eine systemische Infektion hin, wie auch schon für andere hoch pathogene Viren gezeigt
werden konnte (223, 266). R65-trunkNS1 replizierte ebenfalls zu hohen Titern in der Lunge.
Bezüglich der Pathogenität war SC35-wt allerdings eher vergleichbar mit R65-trunkNS1, da
die infizierten Hühner bei diesen beiden Viren erst nach 4 beziehungsweise 5 Tagen
euthanasiert werden mussten. Obwohl SC35-wt in der Literatur als hoch pathogen
beschrieben wird (132) und eine sehr hohe Virusdosis von 1x106 ffu verwendet wurde,
brauchte es vergleichbar lang, bis die Hühner starben. Das könnte daran liegen, dass dieses
Virus aus einem Seehund isoliert worden ist und erst an Hühnerzellen adaptiert werden
musste. Trotz der Unterschiede in der Virulenz der beiden Virusstämme ließ sich aber
feststellen, dass weder SC35-delNS1 noch R65-delNS1 in der Lage war, zu replizieren und
sich auszubreiten. Das zeigt, dass das NS1-Protein auch im Huhn ein wichtiger Virulenzfaktor
ist, ohne den die Viren nicht wachsen und keine Krankheit induzieren können.
Die Tatsache, dass die C-terminal verkürzten NS1-Mutanten in verschiedenen Systemen,
in vitro und in vivo, relativ gut replizieren konnten, kann durch die noch vorhandene RNABindedomäne erklärt werden (114, 187, 214, 251). Der N-Terminus scheint die virale
Replikation zu erleichtern, da gezeigt wurde, dass NS1 als Kofaktor des viralen
Replikationskomplexes dient (45, 124).
5.3 Interferon-Induktion
Da NS1 als IFN-Antagonist in verschiedenen Zellkultursystemen identifiziert wurde (68),
wurde das Zusammenspiel von hoch pathogenen aviären Influenza-A-Viren mit der frühen
angeborenen Immunantwort des Huhns untersucht. Es wurde schon in mehreren Studien
gezeigt, dass C-terminal verkürzte NS1-Mutanten in verschiedenen Zellkultursystemen hoch
attenuiert sind (40, 44, 47, 58, 187, 232). Obwohl die meisten Ergebnisse aus in vitro-
E
98
Diskussion
Experimenten stammen, wird die Reduktion der Virulenz in vivo meist mit einer erhöhten
Induktion an IFN und einer möglichen IFN-Sensitivität in Verbindung gebracht (192). Um zu
untersuchen, ob dies auch für HPAIV gilt, wurde in dieser Arbeit die IFN-Induktion sowohl
in vitro als auch in vivo in verschiedenen Systemen untersucht. Wie erwartet aktivierten die
NS1-Mutanten die Typ I IFN-Gene in CEFs sehr viel stärker als die wt-Viren. Experimente
mit TOCs führten jedoch zu anderen Ergebnissen. Sowohl SC35-wt als auch R65-wt
induzierten ähnliche Mengen an IFN wie die entsprechenden delNS1-Mutanten. Diese
Mengen an IFN schienen auszureichen, um das Wachstum der delNS1-Viren vollständig zu
inhibieren. Die C-terminal trunkierten NS1-Mutanten, sowohl des SC35- als auch des R65Stammes induzierten mehr IFN als die wt- beziehungsweise die delNS1-Mutanten. Diese
Daten zeigen, dass TOCs als Modell viel komplexer sind und dem eigentlichen in vivoSystem näher zu sein scheinen. Neuere Ergebnisse von Reemers et al. deuten allerdings auch
Unterschiede in der zellulären Wirtsantwort nach Influenza-A-Virus-Infektion zwischen
TOCs als ex vivo-System und infizierter Trachea in vivo an (189).
Die IFN-Induktion nach Infektion mit beiden Virusstämmen in vivo wurde sowohl in der
Maus als auch im Huhn untersucht. Die meisten Influenzaviren müssen erst an die Maus
adaptiert werden, da diese kein natürlicher Wirt ist. Deshalb wurden für die SC35-Viren Mxnegative Reporter-Mäuse verwendet, die an Stelle des IFN-β-Gens das Luziferasegen
besitzen. Für die R65-Viren wurden Mx-positive Mäuse verwendet, da bereits für andere
H5N1-Stämme gezeigt wurde, dass sie ohne vorherige Adaptation in diesen Mäusen
replizieren können (57, 141, 241). In beiden Fällen zeigte sich, dass die wt-Viren in der Lage
waren, die IFN-Produktion vollständig zu inhibieren, während die delNS1-Mutanten große
Mengen an IFN induzierten. Dies war zu erwarten, da schon für andere Influenza-A-Stämme
gezeigt wurde, dass sie in der Lage sind, die IFN-Antwort in der Maus zu inhibieren (114,
115). R65-trunkNS1 wies einen intermediären Phänotyp auf. Diese Daten spiegeln vollständig
die Ergebnisse der in vitro-Experimente wieder. Die NS1-Proteine der wt-Viren waren also in
der Lage, in der Maus die Expression von IFN zu inhibieren, wohingegen eine Mutation oder
ein Fehlen dieses Proteins dazu führte, dass die IFN-Antwort nicht mehr inhibiert werden
konnte.
Obwohl im Fall von R65-delNS1 die initiale Infektion auszureichen schien, um eine hohe
IFN-Antwort zu bekommen waren keine Titer in der Lunge messbar. Im Gegensatz dazu
wurde für eine NS1-Deletionsmutante eines mausadaptierten Influenza-A-Stammes gezeigt,
dass eine hohe initiale Replikation zu einer hohen IFN-Antwort in der Mauslunge führt (114).
E
99
Diskussion
Überraschenderweise führten die Versuche mit adulten Hühnern zu einem anderen Ergebnis.
Die wt-Viren induzierten sehr viel mehr IFN in der Lunge und in anderen Organen als die
Mutanten. Die Mutanten mit der kompletten Deletion des NS1-Gens wiesen im Gegensatz
fast überhaupt keine IFN-Induktion auf. Aufgrund der starken Attenuierung schien diese
geringe Menge an IFN auszureichen, um die Replikation und Ausbreitung komplett zu
verhindern. Viren mit C-terminalen NS1-Verkürzungen sollten besser replizieren können als
die Mutanten mit einer kompletten Deletion des NS1-Gens, da sie unter anderem noch die
RNA-Bindedomäne besitzen. Die C-terminal trunkierten NS1-Mutanten induzierten jedoch
ähnlichen Mengen an IFN in infizierten Hühnern wie die wt-Viren, obwohl nach den
Infektionsstudien in CEFs und TOCs zu erwarten gewesen war, dass diese mutanten Viren
viel mehr IFN induzieren. Dass diese Viren in vivo trotzdem nicht mehr IFN induzierten,
zeigt, dass sich das Hühner-Immunsystem anders verhält als das Säugersystem und als aviäre
Zelllinien in vitro. Vielleicht ist die Menge an IFN, welche die wt-Viren induzieren aber auch
schon so hoch, dass keine Steigerung mehr möglich ist. Dies würde auch den Unterschied zu
den TOCs erklären. Auf jeden Fall war das NS1-Protein nicht in der Lage, die IFNGenexpression im Huhn zu inhibieren. Es wurde trotz NS1-Expression eine große Menge IFN
sowohl an der Eintrittsstelle als auch auf systemischen Leveln induziert, was die Hühner
allerdings nicht vor der Infektion schützen konnte. Zumindest in einer bestimmten
Zellpopulation scheint sich die Regulierung der IFN-Signalkaskade anders zu verhalten als im
Säuger. Deshalb wurde als 1. Hypothese aufgestellt, dass dieser bis jetzt noch nicht
identifizierten Zellpopulation, die nach Influenzavirus-Infektion große Mengen an IFN
produziert eventuell ein spezieller Faktor fehlt, der normalerweise für die Wirkung des NS1Proteins essentiell ist. Eine 2. mögliche Hypothese ist, dass diese Zellen einen speziellen
Faktor besitzen, der die Influenzavirus-Replikation in einem sehr frühen Stadium inhibiert.
Wenn in diese Zellen keine produktive Infektion möglich ist, kann das NS1-Protein nicht zu
hohen Leveln akkumulieren und so die IFN-Synthese inhibieren. Überraschenderweise ist bis
heute in keiner Spezies viel über die Art der IFN-produzierenden Zellen in virusinfizierten
Organen bekannt. Man weiß, dass die primären Zielzellen der Influenza-A-Virus-Infektion
und -Replikation zilientragende respiratorische Epithelzellen sind. In aviären Spezies sind des
Weiteren intestinale Epithelzellen und Endothelzellen wichtig (46). Zu späteren Zeitpunkten
sind zusätzlich noch mononukleäre Zellen involviert (53, 99). Über diejenigen Zellen, die
proinflammatorische Zytokine sezernieren und ihre Rolle bei der Pathogenität in Hühnern, die
mit HPAIV infiziert wurden ist allerdings sehr wenig bekannt. Neuere Untersuchungen von
Suzuki et al. deuten an, dass die hohe Pathogenität der asiatischen H5N1-HPAIV mit einer
E
100
Diskussion
extrem schnellen und effizienten Replikation der Viren in Makrophagen und vaskulären
Endothelzellen assoziiert sein könnte. Des Weiteren stellte die Gruppe die Hypothese auf,
dass verschiedene antivirale und inflammatorische Zytokine wie IFN-α, IL-6, IL-8, IL-15 und
IL-18 sehr schnell nach Infektion von Makrophagen produziert werden, während andere wie
IFN-β, aber auch die eben genannten Interleukine von Epithel- oder Endothelzellen produziert
werden. Die effiziente Replikation scheint aufgrund von auftretender Apoptose in den
infizierten Zellen zu einer Zerstörung des Thermoregulationssystems und der angeborenen
Immunantwort zu führen (223). Ein weiterer möglicher Faktor, der zur Virulenz beiträgt, ist,
dass HPAIV nach Infektion von Hühnern Apoptose in vaskulären Endothelzellen in Leber,
Niere und Gehirn induzieren und so zu einem Multi-Organversagen führen (90).
Im Menschen scheinen Epithelzellen und Makrophagen die Zielzellen von H5N1-Viren zu
sein. Es wurde auch beschrieben, dass H5N1-Viren mehr IFN-β und TNF-α in humanen
Makrophagen induzieren als humane H1N1-Stämme. Man spekuliert, dass die aviären Viren
weniger gut an das humane System angepasst sind, was zu einer stärkeren Aktivierung von
RIG-I und IRF-3 führt und infolgedessen die IFN-β-Antwort erhöht (83). Unter den ersten
Genen, die nach viraler Infektion hoch reguliert werden sind auch die TLR-Gene. Für MDV
wurde gezeigt, dass in der Lunge von Hühnern TLR3 und TLR7 in Epithel-, Endothelzellen
und Makrophagen hoch reguliert werden. Die daraufhin ausgeschütteten Zytokine IL-8 und
IL-1β sind in der Lage, eine große Menge an Makrophagen zu rekrutieren, wie es in der
Lunge von MDV-infizierten Hühnern der Fall ist (62). Diese aktivierten Makrophagen sind in
Hühnern eine Quelle für proinflammatorische Zytokine (103, 170)
In Mäusen sind vor allem pDCs, cDCs und Monozyten beziehungsweise Makrophagen für die
IFN-Synthese verantwortlich. Jedoch scheinen nach intranasaler Infektion erst alveolare
Makrophagen und cDCs in der virusinfizierten Lunge die erste Quelle des produzierten IFN
zu sein (260). pDCs werden erst aktiviert, wenn diese Barriere durch das Virus überwunden
wurde (122). Es wurde gezeigt, dass eine H5N1-Infektion von Mäusen zu einer raschen
Einwanderung von Makrophagen und Neutrophilen führt (179). Ebenfalls weisen Studien
darauf hin, dass murine Makrophagen zwar infiziert werden können, aber keine produktive
Infektion unterstützten. Die Infektion führt vielmehr zu einem raschen Apoptoseprozess
innerhalb von 24-48 Stunden. In dieser Zeit können allerdings große Mengen an TNF-a, IL1b, Typ I IFN und vor allem an Chemokinen sezerniert werden, die unter anderem für die
Rekrutierung weiterer Immunzellen verantwortlich sind (99).
Im Huhn wurde gezeigt, dass Makrophagen mit Influenza-A-Viren infiziert werden können,
in diesen Zellen aber die Synthese von IFN unterdrückt ist. Andere Chemokine wie IL-1β und
E
101
Diskussion
IL-6 werden allerdings sezerniert (261). In der Lunge residente Alveolarmakrophagen wie in
der Maus sind jedoch im aviären System nicht vorhanden. Weiter ist zu betonen, dass aviäre
Influenza-A-Viren bei einer natürlichen Infektion fäkal-oral übertragen werden, dass also die
Lunge nicht der Hauptort der Replikation ist (226).
Da das NS1-Protein in der Lage ist, in der infizierten Zelle die IFN-Produktion zu inhibieren,
wurde die Hypothese aufgestellt, dass die Haupt-IFN-Produzenten im Huhn nicht diejenigen
Zellen sind, die infiziert sind. Die ersten Zellen, die in der Lunge von Influenza-A-Viren
infiziert werden, produzieren große Mengen an Virus. In diesen Zellen ist zumindest das wtVirus in der Lage, die IFN-Produktion zu inhibieren. Sobald das Virus sich über die gesamte
Lunge ausgebreitet hat, erreicht es schließlich eine bestimmte Zellpopulation, die schon dort
vorhanden ist oder aber eingewandert sein kann. In dieser speziellen Zellpopulation kann das
NS1-Protein die IFN-Produktion nicht inhibieren. Wahrscheinlich ist keine produktive
Infektion notwendig. Es könnte auch sein, dass überhaupt keine direkte Infektion dieser
Zellen nötig ist, sondern ein bestimmtes Signal ausreicht, um sie zur IFN-Produktion zu
stimulieren. Deshalb ist es essentiell, in weiteren Studien die virusinfizierten und die IFNproduzierenden Zellen zu identifizieren.
Eine weitere Möglichkeit dafür, dass bei Influenzavirus-Infektionen die induzierte IFNMenge die Hühner nicht schützen konnte, ist eine verspätete IFN-Induktion. Im Vergleich
führt eine NDV (Newcastle Disease Virus)-Infektion im Huhn zu einer relativ raschen IFNInduktion (persönliche Kommunikation B. Kaspers, S. Kothlow). Eventuell sind die hoch
pathogenen aviären Influenza-wt-Viren zu schnell und entkommen auf diese Weise dem IFNSystem (231, 65).
5.4 Interferon-Sensitivität
Eine mögliche Erklärung dafür, dass die wt-Viren in Anwesenheit großer Mengen IFN
replizieren können, ohne davon inhibiert zu werden, ist eine hohe NS1-vermittelte IFNResistenz. Aus diesem Grund wurde die IFN-Sensitivität der Viren in verschiedenen
Systemen getestet. Es zeigte sich, dass R65-wt in aviären Zellen sehr IFN-resistent war. Auch
bei großen Mengen an IFN ließ sich nur eine Verzögerung im Wachstum erkennen. Ähnliches
galt auch für R65-trunkNS1. SC35-wt wies ebenfalls eine gewisse IFN-Resistenz in aviären
Zellen auf. Die C-terminal verkürzten NS1-Mutanten ließen sich jedoch durch die IFNBehandlung sowohl in CEFs als auch in den TOCs in ihrem Wachstum inhibieren. Diese
etwas geringere IFN-Resistenz der SC35-Viren ist wahrscheinlich auch der Grund, warum
E
102
Diskussion
SC35-wt eine weniger starke Virulenz in adulten Hühnern aufwies. Das NS1-Protein von
R65-wt weist an Aminosäureposition 92 Glutaminsäure auf. Im Gegensatz dazu findet man
bei SC35-wt an dieser Position Asparaginsäure. Seo et al. konnten zeigen, dass die
Glutaminsäure an Position 92 des NS1 für die Virulenz und die Resistenz gegenüber
antiviralen Zytokinen in Schweinen verantwortlich ist (206). Allerdings wurde auch gezeigt,
dass Alanin an Aminosäureposition 149 des NS1-Proteins wichtig für die Fähigkeit in
Hühnern zu replizieren und Letalität zu verursachen ist. Es wird spekuliert, dass diese
Aminosäure die Menge, Stabilität und Dimerisierungsfähigkeit von NS1 beeinflusst (133).
SC35-wt weist Alanin an dieser Stelle im NS1-Protein auf, was wahrscheinlich zu der
gezeigten Virulenz beiträgt, während R65-wt hier ein Glycin besitzt. Vermutlich tragen
mehrere Faktoren zu der Virulenz und IFN-Sensitivität in verschiedenen Systemen bei.
Die in vivo-Daten im Huhn zeigen, dass es einen großen Unterschied zwischen dem Säugerund dem aviären Immunsystem in Bezug auf Influenzavirus-Infektionen geben muss. In
adulten Hühnern konnte eine IFN-Vorbehandlung die Hühner nicht vor einer letalen Infektion
mit R65-wt schützen. Frühere Studien haben gezeigt, dass ähnlich wie das Gegenstück der
Säuger auch das Hühner-IFN-α prinzipiell in der Lage ist, die Replikation verschiedener
Viren im Huhn zu inhibieren, unter anderem von MDV (92, 131), IBV (infectious bronchitis
virus) (174) und NDV (146). Bei diesen Studien wurde das IFN entweder oral über das
Trinkwasser oder intravenös verabreicht. Des Weiteren wurde gezeigt, dass oral verabreichtes
Hühner-IFN-α den Schwellenwert an Antigen verringert, der für eine Stimulierung der
adaptiven Immunantwort gegen LPAIV benötigt wird. Die Autoren dieser Studie sprechen
von so genannten Super-Sentinel-Hühnern, die durch sehr geringe Level von Antigen
serokonvertieren und die Detektion von LPAIV-Infektionen erleichtern (145). Bei allen
früheren Studien mit NDV, IBV, MDV und Influenzaviren wurden die Auswirkungen der
Infektion durch IFN-Vorbehandlung verbessert. Allerdings wies keines der verwendeten
Viren eine hohe Letalität für Hühner auf. Im Unterschied dazu war R65-wt hoch pathogen für
Hühner und alle Tiere starben innerhalb weniger Tage an der Virus-Infektion. Vielleicht ist
dieses HPAIV zu schnell und zu virulent, um von der Vorbehandlung mit einer hohen Dosis
an IFN in der Replikation inhibiert zu werden. Dafür sprechen auch Studien bei denen gezeigt
wurde, dass sich ein niedrig virulenter H7N3-Influenzavirusstamm sensitiv gegenüber
Hühner-IFN-α in CEFs verhielt (21). Das deutet darauf hin, dass IFN eventuell nur vor
LPAIV oder anderen weniger virulenten Viren schützen kann. Insgesamt kann
geschlussfolgert werden, dass Hühner-IFN-α im Huhn nicht oder nur sehr schlecht gegen
HPAIV zu wirken scheint.
E
103
Diskussion
Im Gegensatz zum Huhn konnten durch die IFN-Vorbehandlung alle Mx-positive Mäuse vor
einer letalen Infektion mit R65-wt geschützt werden. Auch in humanen Lungenepithelzellen
zeigte sich, dass eine IFN-Vorbehandlung einen starken Einfluss auf die Replikationsfähigkeit
von R65-wt und R65-trunkNS1 hatte. Es wurde auch bereits für einen anderen H5N1-Stamm
gezeigt, dass eine IFN-Vorbehandlung Mäuse vor einer letalen Infektion schützen kann (231).
Eine Möglichkeit ist, dass eine IFN-Vorbehandlung von Mäusen nur vor Viren schützt, die
nicht an die Maus adaptiert wurden, und nicht vor Viren, die aufgrund einer guten Adaptation
eine sehr schnelle Replikation aufweisen und bei geringer Infektionsdosis letal sind. Dagegen
sprechen allerdings Studien, bei denen Mäuse durch IFN-Vorbehandlung gegen Infektion mit
einer hohen Dosis eines hoch virulenten, mausadaptierten PR8-Stammes geschützt werden
konnten (65). Zusammen mit den Ergebnissen in Zellkultur kann man schließen, dass HPAIV
im Hühnersystem eine hohe IFN-Resistenz aufweisen, während im Säugersystem IFN die
Zellen vor einer Infektion schützen kann. Das wiederum legt nahe, dass es fundamentale
Unterschiede zwischen dem Säuger- und dem aviären Immunsystem gibt.
Theoretisch könnte es sein, dass das produzierte Hühner-IFN-α keine hohe biologische
Aktivität hatte. Allerdings konnte diese Möglichkeit durch verschiedene Ansätze weitgehend
ausgeschlossen werden. Nach der Herstellung des rekombinanten Hühner-IFN-α wurde durch
einen klassischen antiviralen Assay die Unit-Menge, die zuerst mit einem bekannten Standard
ermittelt wurde, überprüft. Das hergestellte IFN war in der Lage, die Replikation IFNsensitiver Viren, wie VSV zu inhibieren (Daten nicht gezeigt). Außerdem zeigt Abbildung
4.8, dass durch das verwendete IFN Mx (als Marker für ISGs) in TOCs hoch reguliert wurde.
Des Weiteren wies das verwendete IFN auch im Bioassay eine hohe Aktivität auf und die
Hemmung der verschiedenen NS1-Mutanten macht deutlich, dass das Hühner-IFN-α seine
Wirkung auf diesen Zellen entfalten kann. Außerdem wurde nach Applikation in vivo
biologisch aktives IFN im Blutplasma detektiert. Zusätzlich haben Kooperationspartner
gezeigt, dass nach IFN-Applikation in Hühnern Mx als ISG in der Lunge und in der Milz
hoch reguliert wird (persönliche Kommunikation S. Kothlow, B. Kaspers). Es kann also
ausgeschlossen werden, dass das verwendete Hühner-IFN-α keine biologische Aktivität
besaß. Vielmehr deuten die Daten daraufhin, dass HPAIV in Vögeln Strategien entwickelt
haben, durch die sie in der Lage sind, trotz der Anwesenheit großer Mengen an IFN zu
replizieren.
E
104
Diskussion
5.5 Einfluss des NS1-Proteins von R65 auf den Interferon-Signalweg
Eine mögliche Erklärung wie das NS1-Protein von HPAIV die Resistenz gegenüber IFN in
Vögeln vermittelt, ist, dass es die Signalkaskade, die durch IFN induziert wird inhibiert. Für
viele verschiedene virale Faktoren ist bekannt, dass sie in der Lage sind, durch
unterschiedliche Mechanismen die IFN-Signal-Weiterleitung zu inhibieren. Das VP24-Protein
des Ebolavirus bindet z.B. Karyopherin-1 und inhibiert dadurch die nukleäre Akkumulation
von STAT1 (191). Vor kurzem wurde von Pauli et al. gezeigt, dass Influenza-A-Viren die
Typ I IFN-Signalkaskade über die NF-κB-abhängige Induktion der SOCS3 (suppressor of
cytokine signaling)-Expression inhibieren können. SOCS-Proteine sind endogene Inhibitoren
der JAK/STAT-Signalkaskade (172). Bei dieser Studie wurden hauptsächlich verschiedene
humane Zelllinien verwendet. Möglicherweise finden ähnliche Prozesse aber auch im aviären
System statt. Aus diesem Grund wurde in dieser Arbeit überprüft, ob das NS1-Protein von
R65 in der Lage ist, die IFN-Signalkaskade in aviären Zellen zu inhibieren. In der Tat konnte
es die Induktion des Mx-Promotors inhibieren, genau wie auch das NS1-Protein des 1918Stammes, der für die verheerende Epidemie von 1918 verantwortlich war. Im Gegensatz dazu
verhielt sich das NS1-Protein von PR8 wie die C-terminal verkürzten NS1-Mutanten und war
nicht in der Lage, die IFN-Signalkaskade zu inhibieren. Ein ähnliches Verhalten der NS1Proteine von PR8 und des 1918-Stammes wurde auch für humane A549-Zellen beschrieben
(113).
Ein weiterer wichtiger Punkt ist sicherlich die Wirkung der induzierten ISGs im Huhn. In der
Maus ist bereits viel bekannt über die Wirkung verschiedener antiviraler ISGs gegenüber
Influenza-A-Viren. Jedoch sind bisher kaum Untersuchungen durchgeführt worden, bei denen
die Funktionen verschiedenen ISGs speziell im Hühnersystem untersucht wurden. Nur für das
Hühner-Mx-Protein wurde gezeigt, dass es die Replikation von Influenza-A-Viren in Hühnern
nicht zu beeinflussen scheint (11, 12), im Gegensatz zu dem Mx1-Protein der Maus, welches
das Ausmaß der Influenza-A-Resistenz stark beeinflusst (69). Dieser Unterschied in der MxWirkung könnte Abweichungen in der Wirkung des IFN-System des Huhns und der Maus
erklären. Des Weiteren stellt sich die Frage, wie sich andere ISGs, z.B. PKR und OAS, deren
Wirkung im Säuger bekannt ist, im Hühnersystem verhalten, und ob das NS1-Protein in der
Lage ist, diese zu inhibieren. Für Influenza-B-Viren wurde erst kürzlich gezeigt, wie NS1 die
Aktivität von PKR in humanen Zellen inhibiert. Die Kinase wird durch den Export von
viralen Ribonukleoproteinen aus dem Kern aktiviert, aber durch die Bindung des NS1Proteins inhibiert (34). Für Influenza-A-Viren wurde gezeigt, dass NS1-Mutanten in Mx-/--
E
105
Diskussion
und PKR-/--Mäusen zu ähnlichen Titern wie wt-Viren wachsen können (114). Solche Studien
würden entscheidend dazu beitragen, den Einfluss von IFN-Effekten auf die Virulenz und
Pathogenese von HPAIV im Huhn zu klären.
5.6 Ausblick
Die Ergebnisse der vorliegenden Arbeit zeigen, dass HPAIV, die sehr gut an ihren natürlichen
Wirt angepasst sind die IFN-Produktion nicht unbedingt inhibieren müssen, da sie eine hohe
IFN-Resistenz aufweisen. Die Viren sind trotz großer IFN-Mengen, die während der Infektion
produziert werden, in der Lage, zu replizieren und sich auszubreiten, was zu einer
systemischen Infektion und am Ende zum Tod des Wirtes führt. Deshalb ist es wichtig zu
betonen, dass es bezüglich der IFN-Antwort auf Influenzaviren immense Unterschiede
zwischen dem aviären und dem Säugersystem gibt. Diese Informationen könnten nützlich
sein, um Impfstoffe für Hühner zu entwickeln, so dass die Ausbreitung innerhalb der
Hühnerbestände und eine mögliche Übertragung auf andere Spezies wie den Menschen
unterbunden werden. Es gibt mehrere Studien, die C-terminal verkürzte NS1-Mutanten als
Impfstoffe verwendet haben (6, 47, 192, 214, 232). Eine wichtige Voraussetzung für solche
Lebendimpfstoffe ist, dass sie zu hohen Titern in geeigneten Medien produziert werden
können. Auch müssen diese Viren ein gewisses Maß an Attenuierung im Wirt zeigen.
Essentiell dabei ist, dass sie eine gewisse Replikationsfähigkeit zeigen und infolgedessen
immunogen, aber auf keinen Fall krankheitsauslösend sind (232). Verschiedene viel
versprechende Versuche mit unterschiedlichen Virusstämmen sind bisher in der Maus (221)
und im Schwein (192), aber auch in Makaken (6) durchgeführt worden. Auch im Huhn
wurden C-terminal verkürzte NS1-Mutanten auf H5N1-Basis als Impfstoffe mit Erfolg
getestet (221). Bei diesen Versuchen wurde allerdings die multibasische Spaltstelle im
Hämagglutinin entfernt, um zu verhindern, dass sich das Virus im Huhn ausbreitete. Das ist
mit Sicherheit auch der Grund, warum diese H5N1-Mutante nicht letal für Hühner war,
obwohl mit der gleichen Dosis von 1x106 ffu intranasal infiziert wurde (221). Leider wurde
bei keiner dieser Studien die IFN-Anwort nach Infektion mit den C-terminalen NS1-Mutanten
untersucht.
Abschließend kann gesagt werden, dass es große Unterschiede zwischen Zellkultur- und in
vivo-Experimenten beziehungsweise zwischen Säugern und Hühnern gibt. Deshalb ist es
wichtig das Zusammenspiel von aviären Influenza-A-Viren, aber auch anderen aviären Viren,
mit ihrem natürlichen Wirt zu untersuchen.
E
106
Literatur
6. Literatur
1.
2.
3.
4.
5.
6.
7.
8.
9.
10.
11.
12.
13.
14.
15.
16.
17.
Adler, H. E., and A. J. DaMassa. 1979. Toxicity of endotoxin to chicks. Avian Dis
23:174-8.
Amrani, D. L., D. Mauzy-Melitz, and M. W. Mosesson. 1986. Effect of hepatocytestimulating factor and glucocorticoids on plasma fibronectin levels. Biochem J
238:365-71.
Andrejeva, J., K. S. Childs, D. F. Young, T. S. Carlos, N. Stock, S. Goodbourn,
and R. E. Randall. 2004. The V proteins of paramyxoviruses bind the IFN-inducible
RNA helicase, mda-5, and inhibit its activation of the IFN-beta promoter. Proc Natl
Acad Sci U S A 101:17264-9.
Aragon, T., S. de la Luna, I. Novoa, L. Carrasco, J. Ortin, and A. Nieto. 2000.
Eukaryotic translation initiation factor 4GI is a cellular target for NS1 protein, a
translational activator of influenza virus. Mol Cell Biol 20:6259-68.
Bach, E. A., M. Aguet, and R. D. Schreiber. 1997. The IFN gamma receptor: a
paradigm for cytokine receptor signaling. Annu Rev Immunol 15:563-91.
Baskin, C. R., H. Bielefeldt-Ohmann, A. Garcia-Sastre, T. M. Tumpey, N. Van
Hoeven, V. S. Carter, M. J. Thomas, S. Proll, A. Solorzano, R. Billharz, J. L.
Fornek, S. Thomas, C. H. Chen, E. A. Clark, K. Murali-Krishna, and M. G.
Katze. 2007. Functional genomic and serological analysis of the protective immune
response resulting from vaccination of macaques with an NS1-truncated influenza
virus. J Virol 81:11817-27.
Bazzigher, L., A. Schwarz, and P. Staeheli. 1993. No enhanced influenza virus
resistance of murine and avian cells expressing cloned duck Mx protein. Virology
195:100-12.
Bean, W. J., V. S. Hinshaw, and R. G. Webster. 1981. Genetic characterization of
an influenza virus from seals. In D. H. L. Bishop and R-. W. Compans (ed.), The
replication of negative-strand viruses. Elsevier/North-Holland, New York.:363-6367.
Beare, A. S., and R. G. Webster. 1991. Replication of avian influenza viruses in
humans. Arch Virol 119:37-42.
Beilharz, M. W., J. M. Cummins, and A. L. Bennett. 2007. Protection from lethal
influenza virus challenge by oral type 1 interferon. Biochem Biophys Res Commun
355:740-4.
Benfield, C. T., J. W. Lyall, G. Kochs, and L. S. Tiley. 2008. Asparagine 631
variants of the chicken Mx protein do not inhibit influenza virus replication in primary
chicken embryo fibroblasts or in vitro surrogate assays. J Virol 82:7533-9.
Bernasconi, D., U. Schultz, and P. Staeheli. 1995. The interferon-induced Mx
protein of chickens lacks antiviral activity. J Interferon Cytokine Res 15:47-53.
Beutler, B. 2004. Inferences, questions and possibilities in Toll-like receptor
signalling. Nature 430:257-63.
Biron, C. A., K. B. Nguyen, G. C. Pien, L. P. Cousens, and T. P. Salazar-Mather.
1999. Natural killer cells in antiviral defense: function and regulation by innate
cytokines. Annu Rev Immunol 17:189-220.
Bornholdt, Z. A., and B. V. Prasad. 2008. X-ray structure of NS1 from a highly
pathogenic H5N1 influenza virus. Nature 456:985-8.
Bowie, A. G., and I. R. Haga. 2005. The role of Toll-like receptors in the host
response to viruses. Mol Immunol 42:859-67.
Boyd, Y., M. Goodchild, S. Morroll, and N. Bumstead. 2001. Mapping of the
chicken and mouse genes for toll-like receptor 2 (TLR2) to an evolutionarily
conserved chromosomal segment. Immunogenetics 52:294-8.
E
107
18.
19.
20.
21.
22.
23.
24.
25.
26.
27.
28.
29.
30.
31.
32.
33.
34.
Literatur
Burgui, I., T. Aragon, J. Ortin, and A. Nieto. 2003. PABP1 and eIF4GI associate
with influenza virus NS1 protein in viral mRNA translation initiation complexes. J
Gen Virol 84:3263-74.
Capua, I., S. Marangon, M. dalla Pozza, C. Terregino, and G. Cattoli. 2003.
Avian influenza in Italy 1997-2001. Avian Dis 47:839-43.
Capua, I., Mutinelli F. 2001. Low pathogenicity (LPAI) and highly pathogenic
(HPAI) avian influenza in turkeys and chickens. . In CapuaI I, Mutinelli F. (eds), A
Colour Atlas and Text on Avian Influenza, Papi Editore, Bologna:13-20.
Cauthen, A. N., D. E. Swayne, M. J. Sekellick, P. I. Marcus, and D. L. Suarez.
2007. Amelioration of influenza virus pathogenesis in chickens attributed to the
enhanced interferon-inducing capacity of a virus with a truncated NS1 gene. J Virol
81:1838-47.
Chen, W., P. A. Calvo, D. Malide, J. Gibbs, U. Schubert, I. Bacik, S. Basta, R.
O'Neill, J. Schickli, P. Palese, P. Henklein, J. R. Bennink, and J. W. Yewdell.
2001. A novel influenza A virus mitochondrial protein that induces cell death. Nat
Med 7:1306-12.
Chen, Z., Y. Li, and R. M. Krug. 1999. Influenza A virus NS1 protein targets
poly(A)-binding protein II of the cellular 3'-end processing machinery. Embo J
18:2273-83.
Cheung, C. Y., L. L. Poon, A. S. Lau, W. Luk, Y. L. Lau, K. F. Shortridge, S.
Gordon, Y. Guan, and J. S. Peiris. 2002. Induction of proinflammatory cytokines in
human macrophages by influenza A (H5N1) viruses: a mechanism for the unusual
severity of human disease? Lancet 360:1831-7.
Chien, C. Y., Y. Xu, R. Xiao, J. M. Aramini, P. V. Sahasrabudhe, R. M. Krug,
and G. T. Montelione. 2004. Biophysical characterization of the complex between
double-stranded RNA and the N-terminal domain of the NS1 protein from influenza A
virus: evidence for a novel RNA-binding mode. Biochemistry 43:1950-62.
Clemens, M. J., and A. Elia. 1997. The double-stranded RNA-dependent protein
kinase PKR: structure and function. J Interferon Cytokine Res 17:503-24.
Clemens, M. J., and B. R. Williams. 1978. Inhibition of cell-free protein synthesis
by pppA2'p5'A2'p5'A: a novel oligonucleotide synthesized by interferon-treated L cell
extracts. Cell 13:565-72.
Colonna, M., A. Krug, and M. Cella. 2002. Interferon-producing cells: on the front
line in immune responses against pathogens. Curr Opin Immunol 14:373-9.
Compans, R. W., H. Meier-Ewert, and P. Palese. 1974. Assembly of lipidcontaining viruses. J Supramol Struct 2:496-511.
Cook, J. K., J. H. Darbyshire, and R. W. Peters. 1976. The use of chicken tracheal
organ cultures for the isolation and assay of avian infectious bronchitis virus. Arch
Virol 50:109-18.
Crippen, T. L. 2006. The selective inhibition of nitric oxide production in the avian
macrophage cell line HD11. Vet Immunol Immunopathol 109:127-37.
Cummiskey, J. F., J. V. Hallum, M. S. Skinner, and G. A. Leslie. 1973. Persistent
Newcastle disease virus infection in embryonic chicken tracheal organ cultures. Infect
Immun 8:657-64.
Dalloul, R. A., T. W. Bliss, Y. H. Hong, I. Ben-Chouikha, D. W. Park, C. L.
Keeler, and H. S. Lillehoj. 2007. Unique responses of the avian macrophage to
different species of Eimeria. Mol Immunol 44:558-66.
Dauber, B., L. Martinez-Sobrido, J. Schneider, R. Hai, Z. Waibler, U. Kalinke, A.
Garcia-Sastre, and T. Wolff. 2009. Influenza B virus ribonucleoprotein is a potent
activator of the antiviral kinase PKR. PLoS Pathog 5:e1000473.
E
108
35.
36.
37.
38.
39.
40.
41.
42.
43.
44.
45.
46.
47.
48.
49.
50.
Literatur
de Andrade, C. R., C. Ibiapina Cda, N. S. Champs, A. C. de Toledo Junior, and I.
F. Picinin. 2009. Avian influenza: the threat of the 21st century. J Bras Pneumol
35:470-9.
de Veer, M. J., M. Holko, M. Frevel, E. Walker, S. Der, J. M. Paranjape, R. H.
Silverman, and B. R. Williams. 2001. Functional classification of interferonstimulated genes identified using microarrays. J Leukoc Biol 69:912-20.
Der, S. D., Y. L. Yang, C. Weissmann, and B. R. Williams. 1997. A doublestranded RNA-activated protein kinase-dependent pathway mediating stress-induced
apoptosis. Proc Natl Acad Sci U S A 94:3279-83.
Der, S. D., A. Zhou, B. R. Williams, and R. H. Silverman. 1998. Identification of
genes differentially regulated by interferon alpha, beta, or gamma using
oligonucleotide arrays. Proc Natl Acad Sci U S A 95:15623-8.
Digby, M. R., and J. W. Lowenthal. 1995. Cloning and expression of the chicken
interferon-gamma gene. J Interferon Cytokine Res 15:939-45.
Egorov, A., S. Brandt, S. Sereinig, J. Romanova, B. Ferko, D. Katinger, A.
Grassauer, G. Alexandrova, H. Katinger, and T. Muster. 1998. Transfectant
influenza A viruses with long deletions in the NS1 protein grow efficiently in Vero
cells. J Virol 72:6437-41.
Ehrhardt, C., T. Wolff, S. Pleschka, O. Planz, W. Beermann, J. G. Bode, M.
Schmolke, and S. Ludwig. 2007. Influenza A virus NS1 protein activates the
PI3K/Akt pathway to mediate antiapoptotic signaling responses. J Virol 81:3058-67.
Elbers, A. R., G. Koch, and A. Bouma. 2005. Performance of clinical signs in
poultry for the detection of outbreaks during the avian influenza A (H7N7) epidemic
in The Netherlands in 2003. Avian Pathol 34:181-7.
Engelhardt, O. G., E. Ullrich, G. Kochs, and O. Haller. 2001. Interferon-induced
antiviral Mx1 GTPase is associated with components of the SUMO-1 system and
promyelocytic leukemia protein nuclear bodies. Exp Cell Res 271:286-95.
Falcon, A. M., A. Fernandez-Sesma, Y. Nakaya, T. M. Moran, J. Ortin, and A.
Garcia-Sastre. 2005. Attenuation and immunogenicity in mice of temperaturesensitive influenza viruses expressing truncated NS1 proteins. J Gen Virol 86:281721.
Falcon, A. M., R. M. Marion, T. Zurcher, P. Gomez, A. Portela, A. Nieto, and J.
Ortin. 2004. Defective RNA replication and late gene expression in temperaturesensitive influenza viruses expressing deleted forms of the NS1 protein. J Virol
78:3880-8.
Feldmann, A., M. K. Schafer, W. Garten, and H. D. Klenk. 2000. Targeted
infection of endothelial cells by avian influenza virus A/FPV/Rostock/34 (H7N1) in
chicken embryos. J Virol 74:8018-27.
Ferko, B., J. Stasakova, J. Romanova, C. Kittel, S. Sereinig, H. Katinger, and A.
Egorov. 2004. Immunogenicity and protection efficacy of replication-deficient
influenza A viruses with altered NS1 genes. J Virol 78:13037-45.
Fitzgerald, K. A., S. M. McWhirter, K. L. Faia, D. C. Rowe, E. Latz, D. T.
Golenbock, A. J. Coyle, S. M. Liao, and T. Maniatis. 2003. IKKepsilon and TBK1
are essential components of the IRF3 signaling pathway. Nat Immunol 4:491-6.
Fortes, P., A. Beloso, and J. Ortin. 1994. Influenza virus NS1 protein inhibits premRNA splicing and blocks mRNA nucleocytoplasmic transport. Embo J 13:704-12.
Fouchier, R. A., V. Munster, A. Wallensten, T. M. Bestebroer, S. Herfst, D.
Smith, G. F. Rimmelzwaan, B. Olsen, and A. D. Osterhaus. 2005. Characterization
of a novel influenza A virus hemagglutinin subtype (H16) obtained from black-headed
gulls. J Virol 79:2814-22.
E
109
51.
52.
53.
54.
55.
56.
57.
58.
59.
60.
61.
62.
63.
64.
65.
Literatur
Fouchier, R. A., B. Olsen, T. M. Bestebroer, S. Herfst, L. van der Kemp, G. F.
Rimmelzwaan, and A. D. Osterhaus. 2003. Influenza A virus surveillance in wild
birds in Northern Europe in 1999 and 2000. Avian Dis 47:857-60.
Frese, M., G. Kochs, H. Feldmann, C. Hertkorn, and O. Haller. 1996. Inhibition of
bunyaviruses, phleboviruses, and hantaviruses by human MxA protein. J Virol
70:915-23.
Fujisawa, H., S. Tsuru, M. Taniguchi, Y. Zinnaka, and K. Nomoto. 1987.
Protective mechanisms against pulmonary infection with influenza virus. I. Relative
contribution of polymorphonuclear leukocytes and of alveolar macrophages to
protection during the early phase of intranasal infection. J Gen Virol 68 ( Pt 2):42532.
Gack, M. U., R. A. Albrecht, T. Urano, K. S. Inn, I. C. Huang, E. Carnero, M.
Farzan, S. Inoue, J. U. Jung, and A. Garcia-Sastre. 2009. Influenza A virus NS1
targets the ubiquitin ligase TRIM25 to evade recognition by the host viral RNA sensor
RIG-I. Cell Host Microbe 5:439-49.
Gack, M. U., Y. C. Shin, C. H. Joo, T. Urano, C. Liang, L. Sun, O. Takeuchi, S.
Akira, Z. Chen, S. Inoue, and J. U. Jung. 2007. TRIM25 RING-finger E3 ubiquitin
ligase is essential for RIG-I-mediated antiviral activity. Nature 446:916-920.
Gambaryan, A., S. Yamnikova, D. Lvov, A. Tuzikov, A. Chinarev, G. Pazynina,
R. Webster, M. Matrosovich, and N. Bovin. 2005. Receptor specificity of influenza
viruses from birds and mammals: new data on involvement of the inner fragments of
the carbohydrate chain. Virology 334:276-83.
Gao, P., S. Watanabe, T. Ito, H. Goto, K. Wells, M. McGregor, A. J. Cooley, and
Y. Kawaoka. 1999. Biological heterogeneity, including systemic replication in mice,
of H5N1 influenza A virus isolates from humans in Hong Kong. J Virol 73:3184-9.
Garcia-Sastre, A. 2002. Mechanisms of inhibition of the host interferon alpha/betamediated antiviral responses by viruses. Microbes Infect 4:647-55.
Garcia-Sastre, A., A. Egorov, D. Matassov, S. Brandt, D. E. Levy, J. E. Durbin, P.
Palese, and T. Muster. 1998. Influenza A virus lacking the NS1 gene replicates in
interferon-deficient systems. Virology 252:324-30.
Garcia, M. A., J. Gil, I. Ventoso, S. Guerra, E. Domingo, C. Rivas, and M.
Esteban. 2006. Impact of protein kinase PKR in cell biology: from antiviral to
antiproliferative action. Microbiol Mol Biol Rev 70:1032-60.
Gaunson, J. E., C. J. Philip, K. G. Whithear, and G. F. Browning. 2006. The
cellular immune response in the tracheal mucosa to Mycoplasma gallisepticum in
vaccinated and unvaccinated chickens in the acute and chronic stages of disease.
Vaccine 24:2627-33.
Gern, J. E., D. A. French, K. A. Grindle, R. A. Brockman-Schneider, S. Konno,
and W. W. Busse. 2003. Double-stranded RNA induces the synthesis of specific
chemokines by bronchial epithelial cells. Am J Respir Cell Mol Biol 28:731-7.
Gorman, O. T., W. J. Bean, and R. G. Webster. 1992. Evolutionary processes in
influenza viruses: divergence, rapid evolution, and stasis. Curr Top Microbiol
Immunol 176:75-97.
Greenspan, D., P. Palese, and M. Krystal. 1988. Two nuclear location signals in the
influenza virus NS1 nonstructural protein. J Virol 62:3020-6.
Grimm, D., P. Staeheli, M. Hufbauer, I. Koerner, L. Martinez-Sobrido, A.
Solorzano, A. Garcia-Sastre, O. Haller, and G. Kochs. 2007. Replication fitness
determines high virulence of influenza A virus in mice carrying functional Mx1
resistance gene. Proc Natl Acad Sci U S A 104:6806-11.
E
110
66.
67.
68.
69.
70.
71.
72.
73.
74.
75.
76.
77.
78.
79.
80.
81.
82.
83.
Literatur
Gyorfy, Z., A. Ohnemus, B. Kaspers, E. Duda, and P. Staeheli. 2003. Truncated
chicken interleukin-1beta with increased biologic activity. J Interferon Cytokine Res
23:223-8.
Hale, B. G., D. Jackson, Y. H. Chen, R. A. Lamb, and R. E. Randall. 2006.
Influenza A virus NS1 protein binds p85beta and activates phosphatidylinositol-3kinase signaling. Proc Natl Acad Sci U S A 103:14194-9.
Hale, B. G., R. E. Randall, J. Ortin, and D. Jackson. 2008. The multifunctional
NS1 protein of influenza A viruses. J Gen Virol 89:2359-76.
Haller, O., H. Arnheiter, I. Gresser, and J. Lindenmann. 1979. Genetically
determined, interferon-dependent resistance to influenza virus in mice. J Exp Med
149:601-12.
Haller, O., M. Frese, D. Rost, P. A. Nuttall, and G. Kochs. 1995. Tick-borne
thogoto virus infection in mice is inhibited by the orthomyxovirus resistance gene
product Mx1. J Virol 69:2596-601.
Haller, O., G. Kochs, and F. Weber. 2006. The interferon response circuit: induction
and suppression by pathogenic viruses. Virology 344:119-30.
Haller, O., P. Staeheli, and G. Kochs. 2009. Protective role of interferon-induced
Mx GTPases against influenza viruses. Rev Sci Tech 28:219-31.
Harmon, B. G. 1998. Avian heterophils in inflammation and disease resistance. Poult
Sci 77:972-7.
Hatada, E., and R. Fukuda. 1992. Binding of influenza A virus NS1 protein to
dsRNA in vitro. J Gen Virol 73 ( Pt 12):3325-9.
Henzler, D. J., D. C. Kradel, S. Davison, A. F. Ziegler, D. Singletary, P. DeBok, A.
E. Castro, H. Lu, R. Eckroade, D. Swayne, W. Lagoda, B. Schmucker, and A.
Nesselrodt. 2003. Epidemiology, production losses, and control measures associated
with an outbreak of avian influenza subtype H7N2 in Pennsylvania (1996-98). Avian
Dis 47:1022-36.
Herrler, G., H. J. Gross, and R. Brossmer. 1995. A synthetic sialic acid analog that
is resistant to the receptor-destroying enzyme can be used by influenza C virus as a
receptor determinant for infection of cells. Biochem Biophys Res Commun 216:821-7.
Hillier, L. 2004. Sequence and comparative analysis of the chicken genome provide
unique perspectives on vertebrate evolution. Nature 432:695-716.
Hippelainen, M., and A. Naukkarinen. 1990. Effects of local and systemic
immunization on serum antibody titres in splenectomized chickens. APMIS 98:131-6.
Hiscott, J., P. Pitha, P. Genin, H. Nguyen, C. Heylbroeck, Y. Mamane, M.
Algarte, and R. Lin. 1999. Triggering the interferon response: the role of IRF-3
transcription factor. J Interferon Cytokine Res 19:1-13.
Hoffmann, B., M. Beer, C. Schelp, H. Schirrmeier, and K. Depner. 2005.
Validation of a real-time RT-PCR assay for sensitive and specific detection of
classical swine fever. J Virol Methods 130:36-44.
Horimoto, T., and Y. Kawaoka. 1994. Reverse genetics provides direct evidence for
a correlation of hemagglutinin cleavability and virulence of an avian influenza A
virus. J Virol 68:3120-8.
Horisberger, M. A., and K. de Staritzky. 1987. A recombinant human interferonalpha B/D hybrid with a broad host-range. J Gen Virol 68 ( Pt 3):945-8.
Hui, K. P., S. M. Lee, C. Y. Cheung, I. H. Ng, L. L. Poon, Y. Guan, N. Y. Ip, A. S.
Lau, and J. S. Peiris. 2009. Induction of proinflammatory cytokines in primary
human macrophages by influenza A virus (H5N1) is selectively regulated by IFN
regulatory factor 3 and p38 MAPK. J Immunol 182:1088-98.
E
111
84.
85.
86.
87.
88.
89.
90.
91.
92.
93.
94.
95.
96.
97.
98.
99.
100.
Literatur
Hyland, L., R. Webby, M. R. Sandbulte, B. Clarke, and S. Hou. 2006. Influenza
virus NS1 protein protects against lymphohematopoietic pathogenesis in an in vivo
mouse model. Virology 349:156-63.
Ikeda, H., L. J. Old, and R. D. Schreiber. 2002. The roles of IFN gamma in
protection against tumor development and cancer immunoediting. Cytokine Growth
Factor Rev 13:95-109.
Inglis, S. C., T. Barrett, C. M. Brown, and J. W. Almond. 1979. The smallest
genome RNA segment of influenza virus contains two genes that may overlap. Proc
Natl Acad Sci U S A 76:3790-4.
Iqbal, M., V. J. Philbin, and A. L. Smith. 2005. Expression patterns of chicken Tolllike receptor mRNA in tissues, immune cell subsets and cell lines. Vet Immunol
Immunopathol 104:117-27.
Isaacs, A., and J. Lindenmann. 1957. Virus interference. I. The interferon. Proc R
Soc Lond B Biol Sci 147:258-67.
Ito, T., J. N. Couceiro, S. Kelm, L. G. Baum, S. Krauss, M. R. Castrucci, I.
Donatelli, H. Kida, J. C. Paulson, R. G. Webster, and Y. Kawaoka. 1998.
Molecular basis for the generation in pigs of influenza A viruses with pandemic
potential. J Virol 72:7367-73.
Ito, T., Y. Kobayashi, T. Morita, T. Horimoto, and Y. Kawaoka. 2002. Virulent
influenza A viruses induce apoptosis in chickens. Virus Res 84:27-35.
Iwasaki, A., and R. Medzhitov. 2004. Toll-like receptor control of the adaptive
immune responses. Nat Immunol 5:987-95.
Jarosinski, K. W., W. Jia, M. J. Sekellick, P. I. Marcus, and K. A. Schat. 2001.
Cellular responses in chickens treated with IFN-alpha orally or inoculated with
recombinant Marek's disease virus expressing IFN-alpha. J Interferon Cytokine Res
21:287-96.
Jimenez-Garcia, L. F., S. R. Green, M. B. Mathews, and D. L. Spector. 1993.
Organization of the double-stranded RNA-activated protein kinase DAI and virusassociated VA RNAI in adenovirus-2-infected HeLa cells. J Cell Sci 106 ( Pt 1):1122.
Johnson, N. P., and J. Mueller. 2002. Updating the accounts: global mortality of the
1918-1920 "Spanish" influenza pandemic. Bull Hist Med 76:105-15.
Kaiser, P. 2007. The avian immune genome--a glass half-full or half-empty?
Cytogenet Genome Res 117:221-30.
Kamps, B., Hoffmann C, Preiser W. 2006. Influenza Report 2006. Flying Publisher.
Karpala, A. J., K. R. Morris, M. M. Broadway, P. G. McWaters, T. E. O'Neil, K.
E. Goossens, J. W. Lowenthal, and A. G. Bean. 2008. Molecular cloning,
expression, and characterization of chicken IFN -lambda. J Interferon Cytokine Res
28:341-50.
Kash, J. C., T. M. Tumpey, S. C. Proll, V. Carter, O. Perwitasari, M. J. Thomas,
C. F. Basler, P. Palese, J. K. Taubenberger, A. Garcia-Sastre, D. E. Swayne, and
M. G. Katze. 2006. Genomic analysis of increased host immune and cell death
responses induced by 1918 influenza virus. Nature 443:578-81.
Kaufmann, A., R. Salentin, R. G. Meyer, D. Bussfeld, C. Pauligk, H. Fesq, P.
Hofmann, M. Nain, D. Gemsa, and H. Sprenger. 2001. Defense against influenza A
virus infection: essential role of the chemokine system. Immunobiology 204:603-13.
Kawai, T., K. Takahashi, S. Sato, C. Coban, H. Kumar, H. Kato, K. J. Ishii, O.
Takeuchi, and S. Akira. 2005. IPS-1, an adaptor triggering RIG-I- and Mda5mediated type I interferon induction. Nat Immunol 6:981-8.
E
112
101.
102.
103.
104.
105.
106.
107.
108.
109.
110.
111.
112.
113.
114.
115.
116.
Literatur
Kawaoka, Y., S. Krauss, and R. G. Webster. 1989. Avian-to-human transmission of
the PB1 gene of influenza A viruses in the 1957 and 1968 pandemics. J Virol
63:4603-8.
Kerr, I. M., R. E. Brown, and A. G. Hovanessian. 1977. Nature of inhibitor of cellfree protein synthesis formed in response to interferon and double-stranded RNA.
Nature 268:540-2.
Khatri, M., J. M. Palmquist, R. M. Cha, and J. M. Sharma. 2005. Infection and
activation of bursal macrophages by virulent infectious bursal disease virus. Virus Res
113:44-50.
Kida, H., T. Ito, J. Yasuda, Y. Shimizu, C. Itakura, K. F. Shortridge, Y.
Kawaoka, and R. G. Webster. 1994. Potential for transmission of avian influenza
viruses to pigs. J Gen Virol 75 ( Pt 9):2183-8.
Kim, J. A., S. Y. Ryu, and S. H. Seo. 2005. Cells in the respiratory and intestinal
tracts of chickens have different proportions of both human and avian influenza virus
receptors. J Microbiol 43:366-9.
King, P., and S. Goodbourn. 1998. STAT1 is inactivated by a caspase. J Biol Chem
273:8699-704.
Klasing, K. C., and R. K. Peng. 1987. Influence of cell sources, stimulating agents,
and incubation conditions on release of interleukin-1 from chicken macrophages. Dev
Comp Immunol 11:385-94.
Klenk, H. D. 2005. Infection of the endothelium by influenza viruses. Thromb
Haemost 94:262-5.
Klumpp, K., R. W. Ruigrok, and F. Baudin. 1997. Roles of the influenza virus
polymerase and nucleoprotein in forming a functional RNP structure. Embo J
16:1248-57.
Ko, J. H., A. Asano, Y. Kon, T. Watanabe, and T. Agui. 2004. Characterization of
the chicken PKR: polymorphism of the gene and antiviral activity against vesicular
stomatitis virus. Jpn J Vet Res 51:123-33.
Ko, J. H., H. K. Jin, A. Asano, A. Takada, A. Ninomiya, H. Kida, H. Hokiyama,
M. Ohara, M. Tsuzuki, M. Nishibori, M. Mizutani, and T. Watanabe. 2002.
Polymorphisms and the differential antiviral activity of the chicken Mx gene. Genome
Res 12:595-601.
Kobasa, D., S. M. Jones, K. Shinya, J. C. Kash, J. Copps, H. Ebihara, Y. Hatta, J.
H. Kim, P. Halfmann, M. Hatta, F. Feldmann, J. B. Alimonti, L. Fernando, Y. Li,
M. G. Katze, H. Feldmann, and Y. Kawaoka. 2007. Aberrant innate immune
response in lethal infection of macaques with the 1918 influenza virus. Nature
445:319-23.
Kochs, G., A. Garcia-Sastre, and L. Martinez-Sobrido. 2007. Multiple antiinterferon actions of the influenza A virus NS1 protein. J Virol 81:7011-21.
Kochs, G., I. Koerner, L. Thiel, S. Kothlow, B. Kaspers, N. Ruggli, A.
Summerfield, J. Pavlovic, J. Stech, and P. Staeheli. 2007. Properties of H7N7
influenza A virus strain SC35M lacking interferon antagonist NS1 in mice and
chickens. J Gen Virol 88:1403-9.
Kochs, G., L. Martinez-Sobrido, S. Lienenklaus, S. Weiss, A. Garcia-Sastre, and
P. Staeheli. 2009. Strong interferon-inducing capacity of a highly virulent variant of
influenza A virus strain PR8 with deletions in the NS1 gene. J Gen Virol 90:2990-4.
Kogut, M. H., M. Iqbal, H. He, V. Philbin, P. Kaiser, and A. Smith. 2005.
Expression and function of Toll-like receptors in chicken heterophils. Dev Comp
Immunol 29:791-807.
E
113
117.
118.
119.
120.
121.
122.
123.
124.
125.
126.
127.
128.
129.
130.
131.
132.
133.
Literatur
Kogut, M. H., L. Rothwell, and P. Kaiser. 2005. IFN-gamma priming of chicken
heterophils upregulates the expression of proinflammatory and Th1 cytokine mRNA
following receptor-mediated phagocytosis of Salmonella enterica serovar enteritidis. J
Interferon Cytokine Res 25:73-81.
Kogut, M. H., C. Swaggerty, H. He, I. Pevzner, and P. Kaiser. 2006. Toll-like
receptor agonists stimulate differential functional activation and cytokine and
chemokine gene expression in heterophils isolated from chickens with differential
innate responses. Microbes Infect 8:1866-74.
Kotenko, S. V., G. Gallagher, V. V. Baurin, A. Lewis-Antes, M. Shen, N. K. Shah,
J. A. Langer, F. Sheikh, H. Dickensheets, and R. P. Donnelly. 2003. IFN-lambdas
mediate antiviral protection through a distinct class II cytokine receptor complex. Nat
Immunol 4:69-77.
Krauss, S., D. Walker, S. P. Pryor, L. Niles, L. Chenghong, V. S. Hinshaw, and R.
G. Webster. 2004. Influenza A viruses of migrating wild aquatic birds in North
America. Vector Borne Zoonotic Dis 4:177-89.
Krug, R. M., M. Ueda, and P. Palese. 1975. Temperature-sensitive mutants of
influenza WSN virus defective in virus-specific RNA synthesis. J Virol 16:790-6.
Kumagai, Y., O. Takeuchi, H. Kato, H. Kumar, K. Matsui, E. Morii, K. Aozasa,
T. Kawai, and S. Akira. 2007. Alveolar macrophages are the primary interferonalpha producer in pulmonary infection with RNA viruses. Immunity 27:240-52.
Kumar, A., J. Haque, J. Lacoste, J. Hiscott, and B. R. Williams. 1994. Doublestranded RNA-dependent protein kinase activates transcription factor NF-kappa B by
phosphorylating I kappa B. Proc Natl Acad Sci U S A 91:6288-92.
Kuo, R. L., and R. M. Krug. 2009. Influenza a virus polymerase is an integral
component of the CPSF30-NS1A protein complex in infected cells. J Virol 83:1611-6.
Kwon, Y. K., S. J. Joh, M. C. Kim, H. W. Sung, Y. J. Lee, J. G. Choi, E. K. Lee,
and J. H. Kim. 2005. Highly pathogenic avian influenza (H5N1) in the commercial
domestic ducks of South Korea. Avian Pathol 34:367-70.
Laemmli, U. K. 1970. Cleavage of structural proteins during the assembly of the head
of bacteriophage T4. Nature 227:680-5.
Lamb, R. A., and P. W. Choppin. 1979. Segment 8 of the influenza virus genome is
unique in coding for two polypeptides. Proc Natl Acad Sci U S A 76:4908-12.
Landis, H., A. Simon-Jodicke, A. Kloti, C. Di Paolo, J. J. Schnorr, S. SchneiderSchaulies, H. P. Hefti, and J. Pavlovic. 1998. Human MxA protein confers
resistance to Semliki Forest virus and inhibits the amplification of a Semliki Forest
virus-based replicon in the absence of viral structural proteins. J Virol 72:1516-22.
Lazzari, S., and K. Stohr. 2004. Avian influenza and influenza pandemics. Bull
World Health Organ 82:242.
Leveque, G., V. Forgetta, S. Morroll, A. L. Smith, N. Bumstead, P. Barrow, J. C.
Loredo-Osti, K. Morgan, and D. Malo. 2003. Allelic variation in TLR4 is linked to
susceptibility to Salmonella enterica serovar Typhimurium infection in chickens.
Infect Immun 71:1116-24.
Levy, A. M., E. D. Heller, G. Leitner, and I. Davidson. 1999. Effect of native
chicken interferon on MDV replication. Acta Virol 43:121-7.
Li, S. Q., M. Orlich, and R. Rott. 1990. Generation of seal influenza virus variants
pathogenic for chickens, because of hemagglutinin cleavage site changes. J Virol
64:3297-303.
Li, Z., Y. Jiang, P. Jiao, A. Wang, F. Zhao, G. Tian, X. Wang, K. Yu, Z. Bu, and
H. Chen. 2006. The NS1 gene contributes to the virulence of H5N1 avian influenza
viruses. J Virol 80:11115-23.
E
114
134.
135.
136.
137.
138.
139.
140.
141.
142.
143.
144.
145.
146.
147.
148.
149.
150.
Literatur
Lienenklaus, S., M. Cornitescu, N. Zietara, M. Lyszkiewicz, N. Gekara, J.
Jablonska, F. Edenhofer, K. Rajewsky, D. Bruder, M. Hafner, P. Staeheli, and S.
Weiss. 2009. Novel reporter mouse reveals constitutive and inflammatory expression
of IFN-beta in vivo. J Immunol 183:3229-36.
Lindenmann, J. 1964. Inheritance of Resistance to Influenza Virus in Mice. Proc Soc
Exp Biol Med 116:506-9.
Lindenmann, J. 1962. Resistance of mice to mouse-adapted influenza A virus.
Virology 16:203-4.
Loots, K., M. V. Loock, D. Vanrompay, and B. M. Goddeeris. 2006. CpG motifs as
adjuvant in DNA vaccination against Chlamydophila psittaci in turkeys. Vaccine
24:4598-601.
Lowenthal, J. W., P. Staeheli, U. Schultz, M. J. Sekellick, and P. I. Marcus. 2001.
Nomenclature of avian interferon proteins. J Interferon Cytokine Res 21:547-9.
Ludwig, S., U. Schultz, J. Mandler, W. M. Fitch, and C. Scholtissek. 1991.
Phylogenetic relationship of the nonstructural (NS) genes of influenza A viruses.
Virology 183:566-77.
Lynn, D. J., A. T. Lloyd, and C. O'Farrelly. 2003. In silico identification of
components of the Toll-like receptor (TLR) signaling pathway in clustered chicken
expressed sequence tags (ESTs). Vet Immunol Immunopathol 93:177-84.
Maines, T. R., X. H. Lu, S. M. Erb, L. Edwards, J. Guarner, P. W. Greer, D. C.
Nguyen, K. J. Szretter, L. M. Chen, P. Thawatsupha, M. Chittaganpitch, S.
Waicharoen, D. T. Nguyen, T. Nguyen, H. H. Nguyen, J. H. Kim, L. T. Hoang, C.
Kang, L. S. Phuong, W. Lim, S. Zaki, R. O. Donis, N. J. Cox, J. M. Katz, and T.
M. Tumpey. 2005. Avian influenza (H5N1) viruses isolated from humans in Asia in
2004 exhibit increased virulence in mammals. J Virol 79:11788-800.
Maines, T. R., K. J. Szretter, L. Perrone, J. A. Belser, R. A. Bright, H. Zeng, T.
M. Tumpey, and J. M. Katz. 2008. Pathogenesis of emerging avian influenza viruses
in mammals and the host innate immune response. Immunol Rev 225:68-84.
Malathi, K., B. Dong, M. Gale, Jr., and R. H. Silverman. 2007. Small self-RNA
generated by RNase L amplifies antiviral innate immunity. Nature 448:816-9.
Malmgaard, L. 2004. Induction and regulation of IFNs during viral infections. J
Interferon Cytokine Res 24:439-54.
Marcus, P. I., T. Girshick, L. van der Heide, and M. J. Sekellick. 2007. Supersentinel chickens and detection of low-pathogenicity influenza virus. Emerg Infect Dis
13:1608-10.
Marcus, P. I., L. van der Heide, and M. J. Sekellick. 1999. Interferon action on
avian viruses. I. Oral administration of chicken interferon-alpha ameliorates Newcastle
disease. J Interferon Cytokine Res 19:881-5.
Marion, R. M., T. Zurcher, S. de la Luna, and J. Ortin. 1997. Influenza virus NS1
protein interacts with viral transcription-replication complexes in vivo. J Gen Virol 78
( Pt 10):2447-51.
Martin, K., and A. Helenius. 1991. Nuclear transport of influenza virus
ribonucleoproteins: the viral matrix protein (M1) promotes export and inhibits import.
Cell 67:117-30.
Matrosovich, M. N., T. Y. Matrosovich, T. Gray, N. A. Roberts, and H. D. Klenk.
2004. Human and avian influenza viruses target different cell types in cultures of
human airway epithelium. Proc Natl Acad Sci U S A 101:4620-4.
Medzhitov, R., P. Preston-Hurlburt, and C. A. Janeway, Jr. 1997. A human
homologue of the Drosophila Toll protein signals activation of adaptive immunity.
Nature 388:394-7.
E
115
151.
152.
153.
154.
155.
156.
157.
158.
159.
160.
161.
162.
163.
164.
165.
166.
167.
Literatur
Melen, K., L. Kinnunen, R. Fagerlund, N. Ikonen, K. Y. Twu, R. M. Krug, and I.
Julkunen. 2007. Nuclear and nucleolar targeting of influenza A virus NS1 protein:
striking differences between different virus subtypes. J Virol 81:5995-6006.
Merlino, P. G., and J. A. Marsh. 2002. The enhancement of avian NK cell
cytotoxicity by thymulin is not mediated by the regulation of IFN-gamma production.
Dev Comp Immunol 26:103-10.
Meylan, E., J. Curran, K. Hofmann, D. Moradpour, M. Binder, R.
Bartenschlager, and J. Tschopp. 2005. Cardif is an adaptor protein in the RIG-I
antiviral pathway and is targeted by hepatitis C virus. Nature 437:1167-72.
Mibayashi, M., L. Martinez-Sobrido, Y. M. Loo, W. B. Cardenas, M. Gale, Jr.,
and A. Garcia-Sastre. 2007. Inhibition of retinoic acid-inducible gene I-mediated
induction of beta interferon by the NS1 protein of influenza A virus. J Virol 81:51424.
Miettinen, M., T. Sareneva, I. Julkunen, and S. Matikainen. 2001. IFNs activate
toll-like receptor gene expression in viral infections. Genes Immun 2:349-55.
Mo, I. P., M. Brugh, O. J. Fletcher, G. N. Rowland, and D. E. Swayne. 1997.
Comparative pathology of chickens experimentally inoculated with avian influenza
viruses of low and high pathogenicity. Avian Dis 41:125-36.
Nanda, I., C. Sick, U. Munster, B. Kaspers, M. Schartl, P. Staeheli, and M.
Schmid. 1998. Sex chromosome linkage of chicken and duck type I interferon genes:
further evidence of evolutionary conservation of the Z chromosome in birds.
Chromosoma 107:204-10.
Nemeroff, M. E., S. M. Barabino, Y. Li, W. Keller, and R. M. Krug. 1998.
Influenza virus NS1 protein interacts with the cellular 30 kDa subunit of CPSF and
inhibits 3'end formation of cellular pre-mRNAs. Mol Cell 1:991-1000.
Nemeroff, M. E., X. Y. Qian, and R. M. Krug. 1995. The influenza virus NS1
protein forms multimers in vitro and in vivo. Virology 212:422-8.
Neumann, G., T. Noda, and Y. Kawaoka. 2009. Emergence and pandemic potential
of swine-origin H1N1 influenza virus. Nature 459:931-9.
Neumann, U., and E. F. Kaleta. 1975. Detection of Newcastle disease virus in
chicken tracheal organ cultures by the fluorescent antibody technique and by the
embryonated egg method. Avian Pathol 4:227-32.
Newby, C. M., L. Sabin, and A. Pekosz. 2007. The RNA binding domain of
influenza A virus NS1 protein affects secretion of tumor necrosis factor alpha,
interleukin-6, and interferon in primary murine tracheal epithelial cells. J Virol
81:9469-80.
Noah, D. L., K. Y. Twu, and R. M. Krug. 2003. Cellular antiviral responses against
influenza A virus are countered at the posttranscriptional level by the viral NS1A
protein via its binding to a cellular protein required for the 3' end processing of
cellular pre-mRNAS. Virology 307:386-95.
Noda, T., H. Sagara, A. Yen, A. Takada, H. Kida, R. H. Cheng, and Y. Kawaoka.
2006. Architecture of ribonucleoprotein complexes in influenza A virus particles.
Nature 439:490-2.
O'Neill, R. E., J. Talon, and P. Palese. 1998. The influenza virus NEP (NS2 protein)
mediates the nuclear export of viral ribonucleoproteins. Embo J 17:288-96.
Offermann, M. K., J. Zimring, K. H. Mellits, M. K. Hagan, R. Shaw, R. M.
Medford, M. B. Mathews, S. Goodbourn, and R. Jagus. 1995. Activation of the
double-stranded-RNA-activated protein kinase and induction of vascular cell adhesion
molecule-1 by poly (I).poly (C) in endothelial cells. Eur J Biochem 232:28-36.
Olah, I., and B. Glick. 1984. Lymphopineal tissue in the chicken. Dev Comp
Immunol 8:855-62.
E
116
168.
169.
170.
171.
172.
173.
174.
175.
176.
177.
178.
179.
180.
181.
182.
183.
184.
185.
Literatur
Opitz, B., A. Rejaibi, B. Dauber, J. Eckhard, M. Vinzing, B. Schmeck, S.
Hippenstiel, N. Suttorp, and T. Wolff. 2007. IFNbeta induction by influenza A virus
is mediated by RIG-I which is regulated by the viral NS1 protein. Cell Microbiol
9:930-8.
Palese, P. S., M. L. 2007. Orthomyxoviridae: the viruses and their replication. . In
Fields Virology 5th edn.:1647-1689.
Palmquist, J. M., M. Khatri, R. M. Cha, B. M. Goddeeris, B. Walcheck, and J. M.
Sharma. 2006. In vivo activation of chicken macrophages by infectious bursal disease
virus. Viral Immunol 19:305-15.
Pasare, C., and R. Medzhitov. 2004. Toll-like receptors and acquired immunity.
Semin Immunol 16:23-6.
Pauli, E. K., M. Schmolke, T. Wolff, D. Viemann, J. Roth, J. G. Bode, and S.
Ludwig. 2008. Influenza A virus inhibits type I IFN signaling via NF-kappaBdependent induction of SOCS-3 expression. PLoS Pathog 4:e1000196.
Pavlovic, J., T. Zurcher, O. Haller, and P. Staeheli. 1990. Resistance to influenza
virus and vesicular stomatitis virus conferred by expression of human MxA protein. J
Virol 64:3370-5.
Pei, J., M. J. Sekellick, P. I. Marcus, I. S. Choi, and E. W. Collisson. 2001.
Chicken interferon type I inhibits infectious bronchitis virus replication and associated
respiratory illness. J Interferon Cytokine Res 21:1071-7.
Peiris, J. S., Y. Guan, D. Markwell, P. Ghose, R. G. Webster, and K. F.
Shortridge. 2001. Cocirculation of avian H9N2 and contemporary "human" H3N2
influenza A viruses in pigs in southeastern China: potential for genetic reassortment? J
Virol 75:9679-86.
Penniall, R., and J. K. Spitznagel. 1975. Chicken neutrophils: oxidative metabolism
in phagocytic cells devoid of myeloperoxidase. Proc Natl Acad Sci U S A 72:5012-5.
Perez, D. R., W. Lim, J. P. Seiler, G. Yi, M. Peiris, K. F. Shortridge, and R. G.
Webster. 2003. Role of quail in the interspecies transmission of H9 influenza A
viruses: molecular changes on HA that correspond to adaptation from ducks to
chickens. J Virol 77:3148-56.
Perkins, L. E., and D. E. Swayne. 2003. Comparative susceptibility of selected avian
and mammalian species to a Hong Kong-origin H5N1 high-pathogenicity avian
influenza virus. Avian Dis 47:956-67.
Perrone, L. A., J. K. Plowden, A. Garcia-Sastre, J. M. Katz, and T. M. Tumpey.
2008. H5N1 and 1918 pandemic influenza virus infection results in early and
excessive infiltration of macrophages and neutrophils in the lungs of mice. PLoS
Pathog 4:e1000115.
Pestka, S. 1997. The interferon receptors. Semin Oncol 24:S9-18-S9-40.
Pestka, S., J. A. Langer, K. C. Zoon, and C. E. Samuel. 1987. Interferons and their
actions. Annu Rev Biochem 56:727-77.
Philbin, V. J., M. Iqbal, Y. Boyd, M. J. Goodchild, R. K. Beal, N. Bumstead, J.
Young, and A. L. Smith. 2005. Identification and characterization of a functional,
alternatively spliced Toll-like receptor 7 (TLR7) and genomic disruption of TLR8 in
chickens. Immunology 114:507-21.
Pichlmair, A., O. Schulz, C. P. Tan, T. I. Naslund, P. Liljestrom, F. Weber, and
C. Reis e Sousa. 2006. RIG-I-mediated antiviral responses to single-stranded RNA
bearing 5'-phosphates. Science 314:997-1001.
Precious, B., K. Childs, V. Fitzpatrick-Swallow, S. Goodbourn, and R. E.
Randall. 2005. Simian virus 5 V protein acts as an adaptor, linking DDB1 to STAT2,
to facilitate the ubiquitination of STAT1. J Virol 79:13434-41.
Proud, C. G. 1995. PKR: a new name and new roles. Trends Biochem Sci 20:241-6.
E
117
186.
187.
188.
189.
190.
191.
192.
193.
194.
195.
196.
197.
198.
199.
200.
201.
202.
Literatur
Qiu, Y., and R. M. Krug. 1994. The influenza virus NS1 protein is a poly(A)-binding
protein that inhibits nuclear export of mRNAs containing poly(A). J Virol 68:2425-32.
Quinlivan, M., D. Zamarin, A. Garcia-Sastre, A. Cullinane, T. Chambers, and P.
Palese. 2005. Attenuation of equine influenza viruses through truncations of the NS1
protein. J Virol 79:8431-9.
Rebouillat, D., and A. G. Hovanessian. 1999. The human 2',5'-oligoadenylate
synthetase family: interferon-induced proteins with unique enzymatic properties. J
Interferon Cytokine Res 19:295-308.
Reemers, S. S., M. J. Groot Koerkamp, F. C. Holstege, W. van Eden, and L.
Vervelde. 2009. Cellular host transcriptional responses to influenza A virus in chicken
tracheal organ cultures differ from responses in in vivo infected trachea. Vet Immunol
Immunopathol 132:91-100.
Reid, A. H., T. G. Fanning, J. V. Hultin, and J. K. Taubenberger. 1999. Origin
and evolution of the 1918 "Spanish" influenza virus hemagglutinin gene. Proc Natl
Acad Sci U S A 96:1651-6.
Reid, S. P., L. W. Leung, A. L. Hartman, O. Martinez, M. L. Shaw, C.
Carbonnelle, V. E. Volchkov, S. T. Nichol, and C. F. Basler. 2006. Ebola virus
VP24 binds karyopherin alpha1 and blocks STAT1 nuclear accumulation. J Virol
80:5156-67.
Richt, J. A., P. Lekcharoensuk, K. M. Lager, A. L. Vincent, C. M. Loiacono, B.
H. Janke, W. H. Wu, K. J. Yoon, R. J. Webby, A. Solorzano, and A. GarciaSastre. 2006. Vaccination of pigs against swine influenza viruses by using an NS1truncated modified live-virus vaccine. J Virol 80:11009-18.
Roberts, R. M., L. Liu, Q. Guo, D. Leaman, and J. Bixby. 1998. The evolution of
the type I interferons. J Interferon Cytokine Res 18:805-16.
Roberts, W. K., A. Hovanessian, R. E. Brown, M. J. Clemens, and I. M. Kerr.
1976. Interferon-mediated protein kinase and low-molecular-weight inhibitor of
protein synthesis. Nature 264:477-80.
Samuel, C. E. 1993. The eIF-2 alpha protein kinases, regulators of translation in
eukaryotes from yeasts to humans. J Biol Chem 268:7603-6.
Samuelsson, C. V., S. Lienenklaus, P. P. Muller, R. Zawatzky, H. Hauser, and S.
Weiss. 2005. Transformation of mouse fibroblasts alters the induction pattern of type I
IFNs after virus infection. Biochem Biophys Res Commun 335:584-9.
Sato, M., H. Suemori, N. Hata, M. Asagiri, K. Ogasawara, K. Nakao, T. Nakaya,
M. Katsuki, S. Noguchi, N. Tanaka, and T. Taniguchi. 2000. Distinct and essential
roles of transcription factors IRF-3 and IRF-7 in response to viruses for IFNalpha/beta gene induction. Immunity 13:539-48.
Schäfer, W. 1955. Vergleichende sero-immunologische Untersuchung über die Viren
der Influenza und Klassischen Geflügelpest. Zeitschrift Naturforschung 10b:91-91.
Scheiblauer, H., A. P. Kendal, and R. Rott. 1995. Pathogenicity of influenza
A/Seal/Mass/1/80 virus mutants for mammalian species. Arch Virol 140:341-8.
Schneider-Schaulies, S., J. Schneider-Schaulies, A. Schuster, M. Bayer, J.
Pavlovic, and V. ter Meulen. 1994. Cell type-specific MxA-mediated inhibition of
measles virus transcription in human brain cells. J Virol 68:6910-7.
Schultz, U., C. Rinderle, M. J. Sekellick, P. I. Marcus, and P. Staeheli. 1995.
Recombinant chicken interferon from Escherichia coli and transfected COS cells is
biologically active. Eur J Biochem 229:73-6.
Schumacher, B., D. Bernasconi, U. Schultz, and P. Staeheli. 1994. The chicken Mx
promoter contains an ISRE motif and confers interferon inducibility to a reporter gene
in chick and monkey cells. Virology 203:144-8.
E
118
203.
204.
205.
206.
207.
208.
209.
210.
211.
212.
213.
214.
215.
216.
217.
218.
Literatur
Schwarz, H., O. Harlin, A. Ohnemus, B. Kaspers, and P. Staeheli. 2004. Synthesis
of IFN-beta by virus-infected chicken embryo cells demonstrated with specific
antisera and a new bioassay. J Interferon Cytokine Res 24:179-84.
Sekellick, M. J., A. F. Ferrandino, D. A. Hopkins, and P. I. Marcus. 1994. Chicken
interferon gene: cloning, expression, and analysis. J Interferon Res 14:71-9.
Sekellick, M. J., J. W. Lowenthal, T. E. O'Neil, and P. I. Marcus. 1998. Chicken
interferon types I and II enhance synergistically the antiviral state and nitric oxide
secretion. J Interferon Cytokine Res 18:407-14.
Seo, S. H., E. Hoffmann, and R. G. Webster. 2002. Lethal H5N1 influenza viruses
escape host anti-viral cytokine responses. Nat Med 8:950-4.
Seth, R. B., L. Sun, C. K. Ea, and Z. J. Chen. 2005. Identification and
characterization of MAVS, a mitochondrial antiviral signaling protein that activates
NF-kappaB and IRF 3. Cell 122:669-82.
Sheppard, P., W. Kindsvogel, W. Xu, K. Henderson, S. Schlutsmeyer, T. E.
Whitmore, R. Kuestner, U. Garrigues, C. Birks, J. Roraback, C. Ostrander, D.
Dong, J. Shin, S. Presnell, B. Fox, B. Haldeman, E. Cooper, D. Taft, T. Gilbert, F.
J. Grant, M. Tackett, W. Krivan, G. McKnight, C. Clegg, D. Foster, and K. M.
Klucher. 2003. IL-28, IL-29 and their class II cytokine receptor IL-28R. Nat Immunol
4:63-8.
Shin, Y. K., Q. Liu, S. K. Tikoo, L. A. Babiuk, and Y. Zhou. 2007. Influenza A
virus NS1 protein activates the phosphatidylinositol 3-kinase (PI3K)/Akt pathway by
direct interaction with the p85 subunit of PI3K. J Gen Virol 88:13-8.
Sick, C., U. Schultz, U. Munster, J. Meier, B. Kaspers, and P. Staeheli. 1998.
Promoter structures and differential responses to viral and nonviral inducers of
chicken type I interferon genes. J Biol Chem 273:9749-54.
Sick, C., U. Schultz, and P. Staeheli. 1996. A family of genes coding for two
serologically distinct chicken interferons. J Biol Chem 271:7635-9.
Sironi, L., J. L. Williams, A. M. Moreno-Martin, P. Ramelli, A. Stella, H. Jianlin,
S. Weigend, G. Lombardi, P. Cordioli, and P. Mariani. 2008. Susceptibility of
different chicken lines to H7N1 highly pathogenic avian influenza virus and the role of
Mx gene polymorphism coding amino acid position 631. Virology 380:152-6.
Smith, C. K., P. Kaiser, L. Rothwell, T. Humphrey, P. A. Barrow, and M. A.
Jones. 2005. Campylobacter jejuni-induced cytokine responses in avian cells. Infect
Immun 73:2094-100.
Solorzano, A., R. J. Webby, K. M. Lager, B. H. Janke, A. Garcia-Sastre, and J.
A. Richt. 2005. Mutations in the NS1 protein of swine influenza virus impair antiinterferon activity and confer attenuation in pigs. J Virol 79:7535-43.
Spackman, E., D. A. Senne, T. J. Myers, L. L. Bulaga, L. P. Garber, M. L.
Perdue, K. Lohman, L. T. Daum, and D. L. Suarez. 2002. Development of a realtime reverse transcriptase PCR assay for type A influenza virus and the avian H5 and
H7 hemagglutinin subtypes. J Clin Microbiol 40:3256-60.
Staeheli, P., R. Grob, E. Meier, J. G. Sutcliffe, and O. Haller. 1988. Influenza
virus-susceptible mice carry Mx genes with a large deletion or a nonsense mutation.
Mol Cell Biol 8:4518-23.
Staeheli, P., O. Haller, W. Boll, J. Lindenmann, and C. Weissmann. 1986. Mx
protein: constitutive expression in 3T3 cells transformed with cloned Mx cDNA
confers selective resistance to influenza virus. Cell 44:147-58.
Staeheli, P., F. Puehler, K. Schneider, T. W. Gobel, and B. Kaspers. 2001.
Cytokines of birds: conserved functions--a largely different look. J Interferon
Cytokine Res 21:993-1010.
E
119
219.
220.
221.
222.
223.
224.
225.
226.
227.
228.
229.
230.
231.
232.
233.
234.
235.
Literatur
Staeheli, P., and J. G. Sutcliffe. 1988. Identification of a second interferon-regulated
murine Mx gene. Mol Cell Biol 8:4524-8.
Stancato, L. F., M. David, C. Carter-Su, A. C. Larner, and W. B. Pratt. 1996.
Preassociation of STAT1 with STAT2 and STAT3 in separate signalling complexes
prior to cytokine stimulation. J Biol Chem 271:4134-7.
Steel, J., A. C. Lowen, L. Pena, M. Angel, A. Solorzano, R. Albrecht, D. R. Perez,
A. Garcia-Sastre, and P. Palese. 2009. Live attenuated influenza viruses containing
NS1 truncations as vaccine candidates against H5N1 highly pathogenic avian
influenza. J Virol 83:1742-53.
Stieneke-Grober, A., M. Vey, H. Angliker, E. Shaw, G. Thomas, C. Roberts, H.
D. Klenk, and W. Garten. 1992. Influenza virus hemagglutinin with multibasic
cleavage site is activated by furin, a subtilisin-like endoprotease. Embo J 11:2407-14.
Suzuki, K., H. Okada, T. Itoh, T. Tada, M. Mase, K. Nakamura, M. Kubo, and
K. Tsukamoto. 2009. Association of increased pathogenicity of Asian H5N1 highly
pathogenic avian influenza viruses in chickens with highly efficient viral replication
accompanied by early destruction of innate immune responses. J Virol 83:7475-86.
Suzuki, Y. 2005. Sialobiology of influenza: molecular mechanism of host range
variation of influenza viruses. Biol Pharm Bull 28:399-408.
Suzuki, Y., T. Ito, T. Suzuki, R. E. Holland, Jr., T. M. Chambers, M. Kiso, H.
Ishida, and Y. Kawaoka. 2000. Sialic acid species as a determinant of the host range
of influenza A viruses. J Virol 74:11825-31.
Swayne, D. 2008. Avian Influenza. John Wiley & Sons:87-122.
Swayne, D. E. 2007. Understanding the complex pathobiology of high pathogenicity
avian influenza viruses in birds. Avian Dis 51:242-9.
Swayne, D. E., and D.A. Halvorson. 2003. Influenza. In: Y.M. Saif, H.J. Barnes, J.R.
Glisson, A.M. Fadly, L.R. McDougald, and D.E. Swayne. (eds.), Diseases of Poultry
Iowa State University Press: Ames IA:135-160.
Swayne, D. E., and D. L. Suarez. 2000. Highly pathogenic avian influenza. Rev Sci
Tech 19:463-82.
Swayne, D. E. a. D. A. H. 2008. Influenza. In: Y.M. Saif, J.R. Glisson, A.M. Fadly,
L.R. McDougald, and L. Nolan (eds.), Diseases of Poultry Blackwell Publishing:
Ames, JA.
Szretter, K. J., S. Gangappa, J. A. Belser, H. Zeng, H. Chen, Y. Matsuoka, S.
Sambhara, D. E. Swayne, T. M. Tumpey, and J. M. Katz. 2009. Early control of
H5N1 influenza virus replication by the type I interferon response in mice. J Virol
83:5825-34.
Talon, J., M. Salvatore, R. E. O'Neill, Y. Nakaya, H. Zheng, T. Muster, A.
Garcia-Sastre, and P. Palese. 2000. Influenza A and B viruses expressing altered
NS1 proteins: A vaccine approach. Proc Natl Acad Sci U S A 97:4309-14.
Tang, X., J. S. Gao, Y. J. Guan, K. E. McLane, Z. L. Yuan, B. Ramratnam, and
Y. E. Chin. 2007. Acetylation-dependent signal transduction for type I interferon
receptor. Cell 131:93-105.
Taubenberger, J. K., A. H. Reid, R. M. Lourens, R. Wang, G. Jin, and T. G.
Fanning. 2005. Characterization of the 1918 influenza virus polymerase genes. Nature
437:889-93.
Thomis, D. C., and C. E. Samuel. 1995. Mechanism of interferon action:
characterization of the intermolecular autophosphorylation of PKR, the interferoninducible, RNA-dependent protein kinase. J Virol 69:5195-8.
E
120
236.
237.
238.
239.
240.
241.
242.
243.
244.
245.
246.
247.
248.
249.
250.
251.
Literatur
Tomai, M. A., S. J. Gibson, L. M. Imbertson, R. L. Miller, P. E. Myhre, M. J.
Reiter, T. L. Wagner, C. B. Tamulinas, J. M. Beaurline, J. F. Gerster, and et al.
1995. Immunomodulating and antiviral activities of the imidazoquinoline S-28463.
Antiviral Res 28:253-64.
Toth, T. E., and P. B. Siegel. 1993. Cellular defense of the avian respiratory system:
dose-response relationship and duration of response in intratracheal stimulation of
avian respiratory phagocytes by a Pasteurella multocida bacterin. Avian Dis 37:75662.
Treanor, J. J., M. H. Snyder, W. T. London, and B. R. Murphy. 1989. The B allele
of the NS gene of avian influenza viruses, but not the A allele, attenuates a human
influenza A virus for squirrel monkeys. Virology 171:1-9.
Tufveson, G., and G. V. Alm. 1975. Effects of mitogens for mouse B lymphocytes
on chicken lymphoid cells. Immunology 29:697-707.
Tumpey, T. M., C. F. Basler, P. V. Aguilar, H. Zeng, A. Solorzano, D. E. Swayne,
N. J. Cox, J. M. Katz, J. K. Taubenberger, P. Palese, and A. Garcia-Sastre. 2005.
Characterization of the reconstructed 1918 Spanish influenza pandemic virus. Science
310:77-80.
Tumpey, T. M., K. J. Szretter, N. Van Hoeven, J. M. Katz, G. Kochs, O. Haller,
A. Garcia-Sastre, and P. Staeheli. 2007. The Mx1 gene protects mice against the
pandemic 1918 and highly lethal human H5N1 influenza viruses. J Virol 81:10818-21.
Turan, K., M. Mibayashi, K. Sugiyama, S. Saito, A. Numajiri, and K. Nagata.
2004. Nuclear MxA proteins form a complex with influenza virus NP and inhibit the
transcription of the engineered influenza virus genome. Nucleic Acids Res 32:643-52.
Uematsu, S., S. Sato, M. Yamamoto, T. Hirotani, H. Kato, F. Takeshita, M.
Matsuda, C. Coban, K. J. Ishii, T. Kawai, O. Takeuchi, and S. Akira. 2005.
Interleukin-1 receptor-associated kinase-1 plays an essential role for Toll-like receptor
(TLR)7- and TLR9-mediated interferon-{alpha} induction. J Exp Med 201:915-23.
Vaidya, S. A., and G. Cheng. 2003. Toll-like receptors and innate antiviral responses.
Curr Opin Immunol 15:402-7.
van den Broek, M. F., U. Muller, S. Huang, M. Aguet, and R. M. Zinkernagel.
1995. Antiviral defense in mice lacking both alpha/beta and gamma interferon
receptors. J Virol 69:4792-6.
Vilcek, J. 2003. Novel interferons. Nat Immunol 4:8-9.
Vincent, A. L., W. Ma, K. M. Lager, B. H. Janke, R. J. Webby, A. Garcia-Sastre,
and J. A. Richt. 2007. Efficacy of intranasal administration of a truncated NS1
modified live influenza virus vaccine in swine. Vaccine 25:7999-8009.
Vreede, F. T., T. E. Jung, and G. G. Brownlee. 2004. Model suggesting that
replication of influenza virus is regulated by stabilization of replicative intermediates.
J Virol 78:9568-72.
Wan, H., and D. R. Perez. 2006. Quail carry sialic acid receptors compatible with
binding of avian and human influenza viruses. Virology 346:278-86.
Wang, L., D. L. Suarez, M. Pantin-Jackwood, M. Mibayashi, A. Garcia-Sastre, Y.
M. Saif, and C. W. Lee. 2008. Characterization of influenza virus variants with
different sizes of the non-structural (NS) genes and their potential as a live influenza
vaccine in poultry. Vaccine 26:3580-6.
Wang, X., C. F. Basler, B. R. Williams, R. H. Silverman, P. Palese, and A.
Garcia-Sastre. 2002. Functional replacement of the carboxy-terminal two-thirds of
the influenza A virus NS1 protein with short heterologous dimerization domains. J
Virol 76:12951-62.
E
121
252.
253.
254.
255.
256.
257.
258.
259.
260.
261.
262.
263.
264.
265.
266.
267.
Literatur
Weber, S., T. Harder, E. Starick, M. Beer, O. Werner, B. Hoffmann, T. C.
Mettenleiter, and E. Mundt. 2007. Molecular analysis of highly pathogenic avian
influenza virus of subtype H5N1 isolated from wild birds and mammals in northern
Germany. J Gen Virol 88:554-8.
Webster, R. G. 1998. Influenza: an emerging disease. Emerg Infect Dis 4:436-41.
Webster, R. G., W. J. Bean, O. T. Gorman, T. M. Chambers, and Y. Kawaoka.
1992. Evolution and ecology of influenza A viruses. Microbiol Rev 56:152-79.
Webster, R. G., J. Geraci, G. Petursson, and K. Skirnisson. 1981. Conjunctivitis in
human beings caused by influenza A virus of seals. N Engl J Med 304:911.
Webster, R. G., V. S. Hinshaw, W. J. Bean, K. L. Van Wyke, J. R. Geraci, D. J. St
Aubin, and G. Petursson. 1981. Characterization of an influenza A virus from seals.
Virology 113:712-24.
Webster, R. G., and R. Rott. 1987. Influenza virus A pathogenicity: the pivotal role
of hemagglutinin. Cell 50:665-6.
Webster, R. G., M. Yakhno, V. S. Hinshaw, W. J. Bean, and K. G. Murti. 1978.
Intestinal influenza: replication and characterization of influenza viruses in ducks.
Virology 84:268-78.
Weining, K. C., U. Schultz, U. Munster, B. Kaspers, and P. Staeheli. 1996.
Biological properties of recombinant chicken interferon-gamma. Eur J Immunol
26:2440-7.
Wolf, A. I., D. Buehler, S. E. Hensley, L. L. Cavanagh, E. J. Wherry, P. Kastner,
S. Chan, and W. Weninger. 2009. Plasmacytoid dendritic cells are dispensable
during primary influenza virus infection. J Immunol 182:871-9.
Xing, Z., C. J. Cardona, S. Adams, Z. Yang, J. Li, D. Perez, and P. R. Woolcock.
2009. Differential regulation of antiviral and proinflammatory cytokines and
suppression of Fas-mediated apoptosis by NS1 of H9N2 avian influenza virus in
chicken macrophages. J Gen Virol 90:1109-18.
Xu, L. G., Y. Y. Wang, K. J. Han, L. Y. Li, Z. Zhai, and H. B. Shu. 2005. VISA is
an adapter protein required for virus-triggered IFN-beta signaling. Mol Cell 19:72740.
Yang, R. B., M. R. Mark, A. Gray, A. Huang, M. H. Xie, M. Zhang, A. Goddard,
W. I. Wood, A. L. Gurney, and P. J. Godowski. 1998. Toll-like receptor-2 mediates
lipopolysaccharide-induced cellular signalling. Nature 395:284-8.
Yoneyama, M., M. Kikuchi, T. Natsukawa, N. Shinobu, T. Imaizumi, M.
Miyagishi, K. Taira, S. Akira, and T. Fujita. 2004. The RNA helicase RIG-I has an
essential function in double-stranded RNA-induced innate antiviral responses. Nat
Immunol 5:730-7.
Zamarin, D., A. Garcia-Sastre, X. Xiao, R. Wang, and P. Palese. 2005. Influenza
virus PB1-F2 protein induces cell death through mitochondrial ANT3 and VDAC1.
PLoS Pathog 1:e4.
Zhu, Q., H. Yang, W. Chen, W. Cao, G. Zhong, P. Jiao, G. Deng, K. Yu, C. Yang,
Z. Bu, Y. Kawaoka, and H. Chen. 2008. A naturally occurring deletion in its NS
gene contributes to the attenuation of an H5N1 swine influenza virus in chickens. J
Virol 82:220-8.
Zurcher, T., J. Pavlovic, and P. Staeheli. 1992. Nuclear localization of mouse Mx1
protein is necessary for inhibition of influenza virus. J Virol 66:5059-66.
E