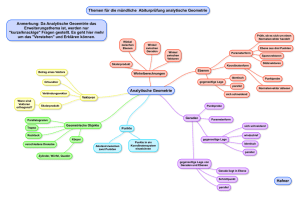
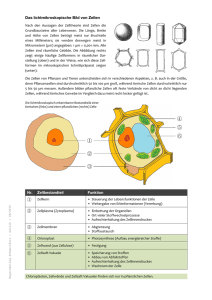
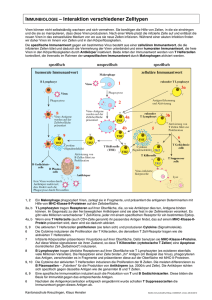
Konstruktion und Charakterisierung Serotyp 5
Werbung

Universität Ulm Abteilung klinische Molekularbiologie Sektion Gentherapie Leiter: Prof. Dr. Stefan Kochanek Konstruktion und Charakterisierung Serotyp 5-basierter adenoviraler Vektoren zur Expression von Modellantigenen für genetische Vakzinierung Dissertation zur Erlangung des Doktorgrades der Medizin der Medizinischen Fakultät der Universität Ulm vorgelegt von Sabine Vöhringer aus Reutlingen 2006 Amtierender Dekan: Prof. Dr. med. Klaus-Michael Debatin 1. Berichterstatter: Prof. Dr. S. Kochanek 2. Berichterstatter: Prof. Dr. T. Mertens Tag der Promotion: 18.12.2008 Meiner geliebten Oma in Erinnerung Inhalt Inhaltsverzeichnis ABKÜRZUNGSVERZEICHNIS .................................................................................III 1 EINLEITUNG ..............................................................................................................1 1.1 Genetische Vakzinierung ............................................................................................1 1.2 Das Immunsystem ......................................................................................................4 1.3 Das Adenovirus ...........................................................................................................6 1.4 Das HBsAg als Modellantigen ................................................................................. 14 1.5 Das Hepatitis B Virus ............................................................................................... 14 1.6 Ein Fusionsprotein als Modellantigen ..................................................................... 16 2 ZIELSETZUNG ......................................................................................................... 17 3 MATERIAL UND METHODEN.............................................................................. 19 3.1 Materialien und Geräte ............................................................................................. 19 3.2 Arbeiten mit Bakterienkulturen................................................................................ 21 3.3 Arbeiten mit Desoxyribonukleinsäuren ...................................................................24 3.4 Arbeiten mit eukaryotischen Zellen .........................................................................30 3.5 Arbeiten mit adenoviralen Vektoren.........................................................................33 3.6 Arbeiten mit Proteinen .............................................................................................42 3.7 Tierexperimentelle Arbeiten.....................................................................................46 4 ERGEBNISSE.............................................................................................................52 4.1 Konstruktion und Charakterisierung der Vektoren..................................................52 4.2 Immunisierungsversuche mit AdHBsAg und AdOVA ............................................ 71 I Inhalt 4.3 Vorläufige Ergebnisse aus weiterführenden Experimenten ....................................85 5 DISKUSSION..............................................................................................................96 5.1 Konstruktion und Charakterisierung ........................................................................96 5.2 Immunisierungsversuche mit AdHBsAg und AdOVA .......................................... 102 5.3 Modifikation von AdHBsAg und Ad1CysHBsAg ...................................................111 5.4 Immunantwort bei PEGylierten und nicht-PEGylierten Vektoren ........................112 5.5 Perspektive...............................................................................................................115 6 ZUSAMMENFASSUNG............................................................................................118 LITERATURVERZEICHNIS .................................................................................... 120 II Abkürzungen Abkürzungsverzeichnis A DNA-Base Adenin, Aminosäure Alanin A549 humane Lungenkarzinom-Zelllinie Abb. Abbildung AB-Komplex Antikörperkomplex für Immunfluoreszenz Ad1Cys cysteinhaltiger adenoviraler Vektor Ad1Cysempty cysteinhaltiger adenoviraler Vektor ohne Transgen Ad1CysHBsAg cysteinhaltiger adenoviraler Vektor, der das HBsAg exprimiert Ad1CysOVA cysteinhaltiger adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP exprimiert Ad1stGFP adenoviraler Vektor, der EGFP exprimiert Ad1stGFP-PEG PEGylierter adenoviraler Vektor, der EGFP exprimiert Ad5 humanes Adenovirus Serotyp 5 Adempty adenoviraler Vektor ohne Transgen AdHBsAg adenoviraler Vektor, der das HBsAg exprimiert AdHBsAg-PEG PEGylierter adenoviraler Vektor, der HBsAg exprimiert AdOVA adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP exprimiert Ag Antigen AIDS „acquired immundeficiency syndrom“ (erworbenes Immundefektsyndrom) APS Ammoniumpersulfat APZ antigenpräsentierende Zelle ATF-2 „activating transcription factor 2” ATP Adenosintriphosphat BALB/c gezüchteter Mausstamm (vollständig: BALB/cAnNCrl) bp Basenpaare BSA bovines Serumalbumin C DNA-Base Cytosin, Aminosäure Cystein III Abkürzungen C57Bl/6 gezüchteter Mausstamm CaCl2 Calciumchlorid CAR Coxsackie-und-Adenovirus-Rezeptor CD „cluster of differentiation“ (Differenzierungsmarker) CIP „calf intestine phosphatase“ (alkalische Kälberdarmphosphatase) CMV hier: Cytomegalovirus „immediate early“ Promotor CPE zytopathischer Effekt CpG Cytidin-Guanin-Dinukleotid (p: Phosphatbindung) CsCl Cäsiumchlorid CTL zytotoxische T-Lymphozyten (CD8-positive T-Zellen) D Aminosäure Aspartat DAB 3’-3’-Diaminobenzidin dCTP Desoxycytidintriphosphat DMSO Dimethylsulfoxid DNA Desoxyribonukleinsäure dNTP Desoxyribonukleotidtriphosphat dsDNA doppelsträngige DNA DTNB 2,2’-dinitro-5,5’-dithiodibenzoesäure DZ dendritische Zelle E „early” (bei Transkriptionseinheiten viraler DNA), Aminosäure Glutamat E. coli Escherichia coli E1 Genregion des humanen Ad5 ECL „enhanced chemoluminescence” EDTA Ethylendiamintetraessigsäure EGFP „enhanced green fluorescent protein“ (modifiziertes, grün fluoreszierendes Protein aus Aequorea victoria) ELISA „enzyme-linked immunosorbent assay“ et al und andere (bezogen auf Literaturangaben im Text) F Aminosäure Phenylalanin IV Abkürzungen FACS „fluorescence activated cell sorter“ (Durchflusszytometer) FCS „fetal calf serum“ (fötales Kälberserum) Fcγ „fragment crystalline“ von IgG FITC Fluoresceinisothiocyanat G DNA-Base Guanin, Aminosäure Glycin g Erdbeschleunigung (9,81 m/s2) h Stunde(n) H2b MHC-Haplotyp H2O Wasser H2O2 Wasserstoffperoxid HBcAg „Hepatitis B Core Antigen“ HBeAg posttranslational verkürzte Form des HBcAg HBsAg „Hepatitis B Surface Antigen“ (Hepatitis B Oberflächenantigen) HBV Hepatitis B Virus HCl Salzsäure HC-Vektor „high capacity“ Vektor (adenoviraler Vektor mit hoher Insertkapazität) HEBS Puffer bestehend aus HEPES, NaCl, Na2HPO4 HEPES N-(2-hydroxyethyl) 1-Piperazino-N-2-Ethansulfonsäure HI-Loop Loop zwischen Domäne H und I HIV humanes Immundefizienzvirus hsp Hitzeschockprotein I Aminosäure Isoleucin i.m. intramuskulär IFNγ Interferon-γ IgG Immunglobulin der Gruppe G ITR „inverted terminal repeat“ (invertierte terminale Sequenzwiederholung) IU internationale Einheiten K Aminosäure Lysin kb Kilobasen V Abkürzungen Kb MHC-Haplotyp KCl Kaliumchlorid kDa Kilodalton L Aminosäure Leucin, „late“ (bei Transkriptionseinheiten viraler DNA) LiCl Lithiumchlorid Lig Ligand m Milli- (= 110-3) M Molar (mol/l) mAK monoklonaler Antikörper max. maximal MCS multiple Klonierungsstelle MEM „modified Eagles medium” MgCl2 Magnesiumchlorid MgSO4 Magnesiumsulfat MHC „major histocompatibility complex“ (Haupthistokompatibilitäts-Molekül) min Minute(n) MOI „multiplicity of infection“ hier: Zahl infektiöser Partikel/Zelle N Aminosäure Asparagin, Normal (bei Pufferlösungen) n Nano- (= 110-9) N52E6 Name der Amniozytenzelllinie zur Adenovirusvektorproduktion Na2HPO4 Dinatriumhydrogenphosphat NaCl Natriumchlorid NaN3 Natriumazid NaOH Natriumhydroxid (hier: Natronlauge) NH4Cl Ammoniumchlorid NHS N-Hydroxysuccinimid NP40 Polyoxyethylen(9)p-t-octylphenol OD optische Dichte 32 radioaktives Phosphorisotop P VI Abkürzungen P Aminosäure Prolin p.a. pro analysi (für analytische Zwecke) p107 Repressorprotein p53 zelluläres Tumorsuppressorprotein pAd1Cysempty Vektorplasmid für die Herstellung von Ad1Cysempty pAd1CysHBsAg Vektorplasmid für die Herstellung von Ad1CysHBsAg pAd1CysOVA Vektorplasmid für die Herstellung von Ad1CysOVA pAd1CysPac Vektorplasmid für die Herstellung von cysteinhaltigen Vektoren pAdempty Vektorplasmid für die Herstellung von Adempty pAdHBsAg Vektorplasmid für die Herstellung von AdHBsAg pAdOVA Vektorplasmid für die Herstellung von AdOVA PAGE Polyacrylamidgelelektrophorese PAMPS „pathogen associated molecular patterns“ PAS Protein A Sepharose pBluescript Plasmid für Klonierungen, Basis für „infektiöse“ Vektorplasmide PBS „phosphat buffered saline“ (phosphatgepufferte Saline) pCI/Ssmall Plasmid, das die Expressionskassette für das HBsAg enthält PCR Polymerase-Kettenreaktion PD-10-Säule Gelfiltrationssäule auf Basis von Sephadex G-25 PEG Polyethylenglykol pEGFP/ cT-OVAkbdbEGFP Plasmid, das für T-OVA-EGFP kodiert pGS66 Vektorplasmid, das für das E1-deletierte Ad5-Genom kodiert pGS70 Plasmid für die Zwischenklonierung in pGS66 pH „pondus hydrogenii“ (Maßeinheit für die Wasserstoffionenkonzentration in einer Lösung) polyA Polyadenylierungssignal pRB Retinoblastom Tumorsuppressor-Protein VII Abkürzungen pSaV1 Plasmid aus einer Zwischenklonierung, das für HBsAg kodiert pSaV2 Plasmid aus einer Zwischenklonierung, das für T-OVA-EGFP kodiert pSaV3 Plasmid aus einer Zwischenklonierung, das für T-OVA-EGFP kodiert Q Aminosäure Glutamin R Aminosäure Arginin RGD Arginin-Glycin-Aspartat-Motiv rpm „revolutions per minute“ (Umdrehungen pro Minute) RPMI Zellkulturmedium (entwickelt am: Roswell Park Memorial Institute) RT Raumtemperatur S Aminosäure Serin s.c. subkutan SDS Natriumdodecylsulfat SH Thiolgruppe (hier: Cysteinrest) SSC Natriumchlorid-Natriumcitrat-Puffer SV40 Simian Virus 40 T DNA-Base Thymin, Aminosäure Threonin Tab. Tabelle TAE Tris-Natriumacetat-EDTA-Puffer TAP Transporter assoziiert mit Antigenpräsentation TBE Tris-Borat-EDTA-Puffer TBS Tris-gepufferte Saline, synonym mit Tris-Saline TCEP Tris-(2-carboxyethyl) phosphin TE Tris-EDTA-Puffer TELT Puffer bestehend aus Tris, EDTA, LiCl, Triton und Lysozym TEMED N,N,N’,N’ – Tetramethylethylendiamin T-OVA-EGFP Fusionsprotein aus Teilen des T-Antigens des Simian Virus 40, des Ovalbumins und EGFP Tris Tris-(hydroxymethyl) aminomethan Tween Polyoxyethylensorbitanmonolaurat VIII Abkürzungen U „unit“ (Einheit der Enzymaktivität) UV Ultraviolettstrahlung V Volt, Aminosäure Valin v/v Volumenprozent vp virale Partikel W Aminosäure Tryptophan w/v Gewichtsprozent µ Mikro- (= 110-6 ) ψ Verpackungssignal IX 1 Einleitung 1 Einleitung 1.1 Genetische Vakzinierung Die Möglichkeit der Impfung zum Schutz vor Infektionskrankheiten gilt als eine der größten Errungenschaften der modernen Medizin. Dabei wird im menschlichen Körper eine spezifische Immunität erzeugt, durch die er im Fall einer natürlichen Infektion mit dem auslösenden Erreger nicht oder nur in milder Form erkrankt. Um dies zu erreichen, stehen mehrere Formen von Impfstoffen zur Verfügung, die sich in ihrer Zusammensetzung sowie der Qualität des ausgelösten Immunschutzes unterscheiden. Die sogenannten Lebendvakzinen bestehen aus attenuierten Erregern der jeweiligen Erkrankung. Durch sie wird eine Immunantwort ausgelöst, die der Antwort bei einer natürlichen Infektion sehr ähnlich ist und sowohl die zelluläre als auch die humorale Komponente des Immunsystems aktiviert. Ihr Nachteil besteht in der Gefahr, durch den Impfstoff an der entsprechenden Krankheit zu erkranken, wodurch sich ihr Einsatz bei schwerwiegenden oder unheilbaren Erkrankungen (z.B. AIDS) verbietet. Dem gegenüber stehen Totimpfstoffe, die abgetötete Erreger enthalten. Bei wesentlich größerer Sicherheit kann mit diesen zwar die humorale Seite des Immunsystems, weniger jedoch der zelluläre Anteil effizient aktiviert werden. Gleiches gilt für neuere Impfstoffe, in denen statt des gesamten Erregers nur noch rekombinante Peptide verwendet werden, die für die Immunantwort verantwortliche Epitope tragen und an ein Trägermolekül gekoppelt sind [1, 29]. Mit diesen Verfahren konnten viele Infektionskrankheiten erfolgreich bekämpft oder, wie im Fall der Pocken, sogar eliminiert werden. Doch die Entwicklung von wirksamen Vakzinen gegen andere schwere und weit verbreitete Erkrankungen wie z.B. Malaria oder AIDS dauert an. Es handelt es sich in diesen Fällen meist um intrazelluläre Erreger, deren immunogene Komponenten längst identifiziert sind [29]. Trotzdem scheint das Immunsystem mit den konventionellen Totimpfstoffen nicht ausreichend stimuliert werden zu können. Insbesondere das Fehlen der zytotoxischen T-Zellen (CTL) wird für das Scheitern verantwortlich gemacht, 1 1 Einleitung da diesen eine wichtige Rolle z.B. in der Kontrolle bestehender HIV-Infektionen zugeschrieben wird [3, 4, 5, 29, 35]. Der Bedarf an neuen Impfstrategien, bei denen bei niedrigem Sicherheitsrisiko auch der zelluläre Anteil der Immunantwort ausreichend aktiviert wird, ist demzufolge sehr groß. Von ihnen erhofft man sich nicht nur Fortschritte in der Bekämpfung von Infektionskrankheiten, sondern auch alternative Verfahren in der Tumortherapie [1, 36, 45]. Ein neuer Ansatz auf diesem Gebiet ist die sogenannte genetische Vakzinierung. Hierbei wird ein Gen, das für ein vom entsprechenden Pathogen stammendes Antigen kodiert, in somatische Zellen des zu immunisierenden Organismus eingebracht. Dahinter steckt die Idee, dass diese Zellen nach Transduktion das Antigen produzieren, es ggf. sezernieren und auf ihrer Oberfläche durch MHC I-Moleküle präsentieren, die wiederum für die Aktivierung der zytotoxischen T-Lymphozyten verantwortlich sind. Die sezernierten Antigenpartikel können in einem zweiten Schritt entweder mit B-Lymphozyten interagieren oder von antigenpräsentierenden Zellen aufgenommen werden, was zusätzlich zur Bildung von Antikörpern und CD4-positiven T-Zellen führt (s. Abschnitt 1.2, S. 4). Auf diesem Weg soll eine starke Immunantwort entstehen, die sowohl die zelluläre als auch die humorale Seite des Immunsystems abdeckt und somit auch zur Prävention von Infektionen mit intrazellulären Erregern geeignet sein könnte. Für den Gentransfer werden derzeit virale und nicht-virale Systeme entwickelt, wobei beide Methoden mit diversen Problemen behaftet sind. Ein typisches Problem nicht-viraler Gentransfervektoren ist ihre niedrige Transfektionseffizienz. Bei viralen Gentransfervektoren überwiegen bei hoher Effizienz Sicherheitsbedenken. Im Fall von auf Adenovirus Serotyp 5 (Ad5) basierenden Vektoren, wie sie für diese Arbeit verwendet wurden, liegt die Schwierigkeit hauptsächlich in einer vorbestehenden Immunität eines Großteils der Bevölkerung gegen Ad5. Sie kann zur Neutralisation der Vektoren durch antiadenovirale Antikörper führen und den Gentransfer erheblich beeinträchtigen [1, 3, 6, 28, 29, 38, 40]. Zudem ist bis jetzt noch keine 2 1 Einleitung gerichtete Transduktion bestimmter Zelltypen möglich, was vor allem im Hinblick auf die Sicherheit der Vektoren ein enormes Defizit darstellt. Im Rahmen dieser Arbeit sollten adenovirale Gentransfervektoren erzeugt werden, die Modellantigene exprimieren und es erlauben, die Wirkung genetisch-chemischer Kapsidmodifikationen (s. Abschnitt 1.3.6, S. 12) auf die genannten Probleme der vorbestehenden Immunität und wenig spezifischen Transduktion vieler Zelltypen zu untersuchen. Als Modellantigene sollten das Hepatitis B Oberflächenantigen (HBsAg), das von transduzierten Zellen sezerniert wird, und ein intrazellulär verbleibendes Fusionsprotein aus Teilen des T-Antigens von SV40, des Ovalbumins und aus EGFP (T-OVA-EGFP) verwendet werden. Die Vektoren sollten alle Voraussetzungen erfüllen, um später Anwendung in in vivoVersuchen zur genetischen Vakzinierung zu finden, in denen die Auswirkungen verschiedener genetisch-chemischer Kapsidmodifikationen auf die Effizienz und das Sicherheitsprofil evaluiert werden können. Zusätzlich sollte ein sowohl qualitativer als auch quantitativer Vergleich der Immunantworten mit denen anderer Gentransfermethoden sowie konventioneller Impfstrategien möglich sein. Die unterschiedlichen Transgene sollten Aufschluss über die Auswirkungen von Sezernierung bzw. intrazellulärem Verbleib des jeweiligen Transgenproduktes auf die Immunantwort geben können. In den folgenden Teilen der Einleitung sollen die Grundlagen des Immunsystems, die Besonderheiten adenoviraler Vektoren, das Prinzip der genetisch-chemischen Kapsidmodifikation sowie die Eignung der Modellantigene in ihren Grundzügen beschrieben werden. 3 1 Einleitung 1.2 Das Immunsystem Das Immunsystem des Körpers besitzt verschiedene Möglichkeiten auf eindringende Fremdkörper zu reagieren. Hierbei unterscheidet man zwischen der angeborenen und der adaptiven Immunantwort. Die angeborene Antwort setzt unmittelbar nach Erregerkontakt ein und umfasst sämtliche unspezifischen Bekämpfungsmechanismen. Hierzu gehören neben antibakteriellen Substanzen (z.B. Lysozym) und natürlichen Killerzellen u.a. auch Makrophagen. Diese erkennen zunächst Fremdantigene über bestimmte molekulare Strukturen („PAMPS“ = pathogen associated molecular patterns) wie beispielsweise Lipopolysaccharide oder unmethylierte CpG-Motive der Pathogen-DNA. Daraufhin erfolgt eine Aufnahme der Fremdkörper durch Phago- bzw. Pinozytose und/oder über Rezeptoren (z.B. Scavenger-, Mannan-, oder Toll-like-Rezeptor). Die anschließende Ausschüttung von Interleukinen und dem Tumor-Nekrose-Faktor-α induziert u.a. eine Akut-Phase-Reaktion der Leber. Über die Präsentation von Fremdkörper-Peptiden auf MHC II-Komplexen besteht eine Verknüpfung zur adaptiven Komponente der Immunantwort (s.u.). Die adaptive Antwort bildet sich spezifisch für jeden einzelnen Erreger und kann deswegen bei Erstkontakt nur verzögert reagieren. Zu ihren Effektorzellen zählen u.a. die zytotoxischen T-Lymphozyten, die T-Helferzellen und die B-Lymphozyten. Die Aktivierung CD8-positiver, zytotoxischer T-Lymphozyten kommt durch Kontakt mit Fremdpeptiden zustande, die auf MHC I-Komplexen präsentiert werden. Diese MHC IKomplexe sind auf allen Körperzellen vorhanden. Sie präsentieren Peptide zytoplasmatischer Proteine, die sowohl fremden als auch zelleigenen Ursprungs sein können. Die Peptide entstehen durch Degradation der Proteine in einem Proteasomenkomplex und gelangen anschließend durch zwei ATP-abhängige Transporter (TAP-1, TAP-2) ins endoplasmatische Retikulum. Dort werden leere MHC I-Moleküle mit den Peptiden beladen, zur Zellmembran transportiert und in diese integriert. Durch Interaktion des beladenen Komplexes mit einer CD8-positiven T-Zelle, die spezifisch für das jeweilige präsentierte Peptid ist, kommt es zu 4 1 Einleitung deren Aktivierung und Proliferation. Daraufhin werden Zellen, die das Fremdpeptid präsentieren, durch direkten Kontakt oder Perforin-Ausschüttung lysiert. Um CD4-positive T-Helferzellen zu aktivieren, müssen Fremdpeptide von MHC IIKomplexen präsentiert werden, die vor allem auf antigenpräsentierenden Zellen (z.B. Makrophagen, B-Lymphozyten, dendritische Zellen) vorhanden sind. Kommt es zur Aufnahme eines Fremdkörpers durch beispielsweise Makrophagen, so befindet sich dieser zunächst im sog. Phagosom. Durch Verschmelzung mit einem Lysosom zum Phagolysosom erfolgt eine Ansäuerung des Milieus, was wiederum eine Aktivierung von Cathepsin-Proteasen, die aus dem Fremdkörper Peptide generieren, zur Folge hat. Die Assoziation dieser Peptide mit MHC II-Molekülen erfolgt ebenfalls im sauren Vesikel. Nach dem Transport zur Zellmembran kann eine peptid-spezifische CD4-positive T-Helferzelle über ihren T-Zell-Rezeptor mit dem beladenen MHC II-Komplex in Interaktion treten und dadurch aktiviert werden. Diese aktivierten T-Lymphozyten wirken über die Ausschüttung von Zytokinen u.a. auf die Antikörperantwort der B-Zellen (s.u.). B-Lymphozyten, die für die Produktion von Antikörpern zuständig sind, können Fremdkörper auch in löslicher Form erkennen. Nach Bindung an den spezifischen B-ZellRezeptor wird der Fremdkörper aufgenommen und wie in Makrophagen (s.o.) prozessiert. Anschließend werden die generierten Peptide auf MHC II-Komplexen präsentiert. Dadurch kommt es zu einer Erkennung durch aktivierte T-Helferzellen und einer Interaktion zwischen B-Zelle und T-Helferzelle. Das führt zur Differenzierung der B-Zelle in eine Plasmazelle, zu deren klonaler Expansion und zur Produktion von Antigen-spezifischen Antikörpern. Diese Antikörper können neben der Neutralisation fremder Partikel auch deren Opsonisierung bewirken, in deren Folge u.a. gesteigerte Phagozytose der Antigen-Antikörper-Komplexe durch Bindung an den Fcγ-Rezeptor von Makrophagen auftreten kann. Die adaptive Komponente des Immunsystems beinhaltet auch das sog. „immunologische Gedächtnis,“ d.h. die Fähigkeit, Informationen über den erfolgreich bekämpften Erreger zu speichern und bei erneuter Konfrontation so schnell wieder abzurufen, dass keine Erkrankung mehr eintritt. Diese Funktion wird u.a. durch T- und B-Gedächtniszellen über einen noch nicht vollständig verstandenen Mechanismus vermittelt. 5 1 Einleitung Das Ziel einer Impfung zum Schutz vor einer Infektionskrankheit ist die Anregung der adaptiven Komponente des Immunsystems, so dass der betreffende Erreger im Fall einer natürlichen Infektion ohne Verzögerung erkannt und bekämpft werden kann. In der Tumortherapie sollen die induzierten adaptiven Mechanismen, insbesondere die spezifischen zytotoxischen T-Lymphozyten, eine Rolle in der Bekämpfung bereits bestehender Tumoren spielen. 1.3 Das Adenovirus 1.3.1 Allgemeines Das Adenovirus gehört zur Familie der Adenoviridae und ist ein hüllenloses Virus mit einem Durchmesser von ca. 70-100 nm. Seitdem 1953 das erste Adenovirus aus adenoidem Gewebe isoliert wurde, wurden über 50 Serotypen des humanen Adenovirus entdeckt und u.a. auf der Basis ihrer hämagglutinierenden Eigenschaften und aufgrund von Sequenzvergleichen in sechs verschiedene Spezies eingeteilt. Bestimmten Serotypen können typische Krankheitsbilder zugeordnet werden, zu denen respiratorische Infekte, Keratokonjunktivitiden und Gastroenteritiden gehören; auch seltene Fälle von hämorrhagischer Zystitis und Meningoenzephalitis wurden beschrieben [34]. Der für gentherapeutische Zwecke hauptsächlich verwendete Serotyp 5 gehört zur Spezies C der Adenoviren (Genus Mastadenoviridae) und ist überwiegend für harmlose respiratorische Infekte verantwortlich. Die Durchseuchung mit Adenoviren beginnt im frühen Kindesalter und beträgt für Serotyp 5 in Deutschland ca. 50%. 1.3.2 Struktur und genomische Organisation Das Kapsid des Adenovirus ist ikosaedrisch aus verschiedenen Proteinen aufgebaut. Mit 240 Homotrimeren ist das Hexonkapsomer am stärksten vertreten. Es bildet nahezu die 6 1 Einleitung komplette Oberfläche und wird von den Proteinen IIIa, VI, VIII und IX stabilisiert. Das Penton-Protein an den zwölf Scheitelpunkten des Ikosaeders bildet die Basis für die zwölf Fiber-Homotrimere, die antennenartig von der Virusoberfläche abstehen und für die Bindung an den Coxsackie-und-Adenovirus-Rezeptor (CAR) verantwortlich sind. Das adenovirale Genom ist doppelsträngig und linear und weist eine Größe von 36000 Basenpaaren (bp) auf. Es wird eingeteilt in frühe (E = early) und späte (L = late) Transkriptionseinheiten, abhängig vom Zeitpunkt ihrer Aktivierung relativ gesehen zum Zeitpunkt des Zelleintritts. Den einzelnen Regionen können Proteine zugeordnet werden, deren jeweilige Funktionen im Replikationszyklus gut bekannt sind. Die beiden E1A-Proteine, auch als trans-Aktivatoren bezeichnet, aktivieren die Transkription der anderen viralen Gene und verändern durch Bindung an verschiedene zelluläre Proteine (z.B. pRB, p107, ATF-2) die Regulation des Zellzyklus so, dass ein Übergang in die S-Phase erreicht wird. Die E1B-Proteine unterstützen diese Funktion und verhindern gleichzeitig die Apoptose der infizierten Zelle. Die drei Produkte der E2-Region, unter anderem eine DNAPolymerase, sind direkt an der Replikation der viralen DNA beteiligt, während E3 für die Modulation der körpereigenen Immunantwort zuständig ist. Die späten Regionen kodieren vor allem für Kapsidproteine [34]. Sowohl am Anfang als auch am Ende des DNA-Stranges befinden sich invertierte Sequenzwiederholungen (ITRs). Diese beinhalten den Replikationsursprung. Am linken Ende folgt auf die ITR das Verpackungssignal ψ, das für die Verpackung der DNA beim Zusammenbau der Viruspartikel am Ende der Replikation essentiell ist. Der Doppelstrang ist an beiden Enden kovalent mit dem terminalen Protein verknüpft. Im Kapsid liegt die DNA in chromatinähnlicher Struktur vor, bei der das sog. Protein VII eine histon-ähnliche Funktion erfüllt. 7 1 Einleitung 1.3.3 Der natürliche Infektionszyklus des Adenovirus Ein Infektionszyklus dauert 36 bis 48 Stunden und teilt sich in eine frühe und eine späte Phase ein. Die frühe Phase beginnt mit dem Anheften des Virus an die Zielzelle durch die Bindung der Knob-Domäne des Fiber-Proteins an den Coxsackie-und-Adenovirus-Rezeptor. Die anschließende Aufnahme des Viruspartikels in die Zelle durch rezeptorvermittelte Endozytose wird über die zusätzliche Interaktion eines sog. RGD-Motivs der Pentonbasis mit αv-Integrinen auf der Zelloberfläche vermittelt [9, 41, 42]. Nach Ansäuerung und partieller Zerlegung entkommt das Adenovirus aus dem Endosom und wandert mit Unterstützung des Zytoskeletts zu den Kernporen, wo die virale DNA importiert wird. Im Zellkern wird diese DNA beginnend bei der E1-Region transkribiert. Deren Genprodukte wiederum aktivieren die Transkription der anderen viralen Gene (s. Abschnitt 1.3.2, S. 6), was zur Synthese von notwendigen Enzymen wie z.B. einer DNA-Polymerase führt, die für die Replikation der viralen DNA benötigt wird. In der späten Phase, nach Replikation der DNA, erfolgt die Synthese der adenoviralen Strukturproteine, die schließlich in den Zusammenbau der neuen viralen Partikel im Zellkern mündet. 1.3.4 Adenoviren als Gentransfervektoren Das Adenovirus besitzt einige Vorzüge, durch die es sich gut als Genfähre eignet. Diese sind vor allem für den Serotyp 5 gesichert, der überwiegend für gentherapeutische Zwecke verwendet wird. Das Virus hat ein relativ stabiles Genom, das leicht manipulierbar ist und im Falle einer Infektion nicht oder nur in sehr geringem Maße in das Genom der Wirtszelle integriert. Es infiziert effizient sowohl ruhende und postmitotische als auch proliferierende Zellen, ist unter Zellkultur-Bedingungen anzüchtbar und kann in großen Mengen produziert werden. Die Erkrankungen, die durch das Adenovirus ausgelöst werden, sind in den meisten Fällen nicht 8 1 Einleitung besonders schwer und gut therapierbar, was aus Gründen der Sicherheit sehr wichtig ist [1, 7, 29, 39, 41]. Platz für den Einbau eines Transgens in das Vektorgenom wird durch Deletion der E1-Region geschaffen. Die zugehörigen Gene E1A und E1B sind für die Replikation des Virus essentiell und können somit bei Gentransfervektoren, die nicht zu einer produktiven Infektion befähigt sein sollen, deletiert werden. Diese Vektoren, die durch die E1- und eventuell zusätzliche E3Deletion Raum für die Aufnahme von DNA einer Größe von bis zu 8 Kilobasen (kb) bieten, werden Erstgenerationsvektoren genannt. Sie können in Zelllinien, die die E1-Genprodukte trans-komplementieren, erzeugt werden. Beispielhaft seien hier 293- oder N52E6-Zellen genannt [30]. Durch die zusätzliche Deletion von E2 und/oder E4 entstanden die Zweitgenerationsvektoren, bis es schließlich gelang, durch Deletion aller Gene die sogenannten High-Capacity- (HC) Vektoren zu konstruieren [13]. Diese enthalten nur noch die invertierten terminalen Sequenzwiederholungen und das Verpackungssignal. Der restliche Platz kann zur Aufnahme von DNA bis zu einer Größe von 36 kb genutzt werden [12, 41]. Für die Produktion von HC-Vektoren wird zusätzlich ein Helfervirus-System benötigt [12, 30, 41]. 1.3.5 Adenovirale Vektoren als genetische Vakzine In verschiedenen Experimenten wurde die Eignung adenoviraler Vektoren für genetische Vakzinierung demonstriert. Sie wurden u.a. in Versuchen zur Entwicklung einer Vakzine gegen das Humane Immunschwäche Virus (HIV) eingesetzt [3, 4, 5, 19, 35]. Hierbei führte die Immunisierung von Primaten zu einer zellulären und humoralen Immunantwort, durch die eine nachfolgende Infektion mit HIV wesentlich besser unter Kontrolle gehalten werden konnte, als dies bei nicht-immunisierten Tieren der Fall war. Der Vergleich adenoviraler Vektoren mit anderen Gentransfersystemen (z.B. modifiziertes Ankara Virus oder PlasmidDNA) zeigte ihre deutliche Überlegenheit. 9 1 Einleitung Zu diesen positiven Erfahrungswerten kommt, dass Eigenschaften, die die Anwendung der Vektoren in der Therapie genetischer Erkrankungen limitieren, bei Immunisierungsversuchen einen Vorteil bieten können. Die transiente Expression des Transgens in transduzierten Zellen reicht aus, um eine Immunantwort auszulösen. Gleichzeitig ist dies ein Sicherheitsfaktor, da keine Spätfolgen durch eine eventuelle Integration des Vektors in das Genom der Wirtszelle zu erwarten sind [29]. Die Immunogenität der adenoviralen Kapsidproteine bewirkt einen Adjuvanseffekt, der zur Verstärkung der Immunantwort beitragen kann [22]. Die Addition eines zusätzlichen Stoffes als Adjuvans könnte somit auch im Hinblick auf eine spätere Vakzine überflüssig werden. Wird ein adenoviraler Vektor zur genetischen Vakzinierung verwendet, so geht man davon aus, dass nach Applikation eines Vektors verschiedene Zelltypen transduziert werden, die anschließend das durch das Transgen kodierte Protein produzieren. Durch Präsentation einzelner Peptide dieses Proteins auf MHC I-Molekülen soll es zur Aktivierung Transgenspezifischer zytotoxischer T-Lymphozyten kommen. Die mögliche Sezernierung des Proteins führt zu Kontakt mit B-Lymphozyten und damit zur Produktion von Antikörpern gegen das Transgen. Bei Aufnahme des Proteins durch Makrophagen und andere antigenpräsentierende Zellen kommt es zur Präsentation auf MHC I („Cross presentation“)- und MHC IIKomplexen [37] und dadurch u.a. zur Stimulation CD4-positiver T-Lymphozyten. Die Transduktion dendritischer Zellen könnte zur gleichzeitigen MHC I- und MHC IIPräsentation des produzierten Proteins [1] und zu einer Unterstützung der Immunantwort in allen genannten Bereichen führen, wobei nicht hinreichend geklärt ist, wie gut Ad5-Vektoren dendritische Zellen in vivo transduzieren können (s. Abb. 1.1, S. 11). 10 1 Einleitung Transgen-exprimierender Vektor Intramuskuläre Injektion DZ * Transduktion z.B. einer Muskelzelle oder eines Fibroblasten Transduktion einer dendritischen Zelle APZ Präsentation auf MHC I T Interaktion mit CD8+ T-Zelle Aufnahme des Proteins durch APZ Proteinsynthese + Sezernierung B Interaktion von Protein und B-Zelle ** APZ Präsentation auf MHC II Lyse infizierter Zellen und klonale Expansion von CD8+ T-Zellen Antikörperproduktion Aktivierung von CD4+ T-Zellen Abbildung 1.1 Möglichkeiten der Antigenpräsentation nach genetischer Vakzinierung Nach intramuskulärer Injektion erfolgt eine Transduktion verschiedener Zelltypen durch den Vektor. Hierbei kann es sich beispielsweise um Muskelzellen, Fibroblasten oder dendritische Zellen (DZ) handeln. Diese Zellen produzieren daraufhin das durch das Transgen kodierte Protein. Wird das Protein sezerniert, führt dies durch direkten Kontakt zu einer Aktivierung von B-Zellen und damit zur Bildung von Antikörpern. Gleichzeitig erfolgt eine Präsentation von Bruchstücken des Proteins auf MHC I-Komplexen der jeweiligen Zellen, was wiederum zytotoxische, CD8-positive (CD8+) T-Zellen aktiviert. Bei Aufnahme des Proteins durch antigenpräsentierende Zellen (APZ) kommt es zur Degradation und Präsentation auf MHC II- und MHC IKomplexen [37]. Dies führt zu einer zusätzlichen Aktivierung von CD4-positiven (CD4+) T-Helfer-Zellen. Die direkte Transduktion von dendritischen Zellen führt zur Präsentation von de novo synthetisierten Proteinen auf MHC I-(*) und MHC II-Komplexen [1] und von prozessierten Vektorkapsidproteinen auf MHC II-Komplexen (**). (MHC: Haupthistokompatibilitäts-Molekül; CD: Differenzierungsmarker) 11 1 Einleitung 1.3.6 Genetische und chemische Kapsidmodifikation Eine Vielzahl unterschiedlicher Zelltypen exprimiert CAR und αv-Integrine. Im Hinblick auf das Sicherheitsprofil adenoviraler Vektoren wäre es jedoch wünschenswert, wenn genau determiniert werden könnte, welche Zellen transduziert werden. Gleichzeitig gibt es schlecht transduzierbare Zellen, deren Transduktion unter Umständen stärkere Immunantworten durch effizientere Antigenpräsentation o.ä. bewirken würde (evtl. dendritische Zellen). Aus diesen Gründen wird seit langem versucht, den natürlichen Tropismus adenoviraler Vektoren zu verändern und damit eine gerichtete Transduktion gewünschter Zellen zu erreichen. Ein Ansatz auf diesem Gebiet ist beispielsweise das genetische Einfügen peptidischer Ligandmotive in den HI-Loop, einen kleinen gut exponierten Teil des Kapsids. Dazu zählt u.a. die Insertion von RGD-Motiven [42], um die Transduktion von Zellen ohne CAR, aber mit αv-Integrinen zu verbessern oder das Einfügen diverser anderer Liganden, welche an für den Ziel-Zelltyp spezifische Rezeptoren binden [1, 9]. Außerdem wurden verschiedene Fusionsproteine z.B. aus einer löslichen Form von CAR und spezifischen Liganden konstruiert, die als Adaptermolekül zwischen Vektor und Zielzelle fungieren sollten [2]. Erwähnt sei der Versuch von Pereboev et al, durch Konstruktion eines Adaptermoleküls aus CAR und dem Liganden für CD40 die Transduktion von dendritischen Zellen zu verbessern [25]. Um das Problem der oftmals vorbestehenden Immunität der Bevölkerung in Form neutralisierender Antikörper gegen Ad5 zu umgehen, wird neben der Verwendung verschiedener anderer Serotypen des humanen Adenovirus [40] und dem Einsatz tierischer Adenoviren [28] auch die genetische oder chemische Modifikation des Kapsids diskutiert, die eine Erkennung des Vektors durch vorhandene Antikörper vermeiden soll. Das Problem vorhandener Antikörper gegen das adenovirale Kapsid ergibt sich auch bei der mehrmaligen Injektion eines Impfstoffes, die in den meisten Impfprotokollen vorgesehen ist. Sie werden, sofern sie nicht ohnehin vorhanden sind (vorbestehende Immunität, s.o.), nach der ersten Vektorinjektion gebildet. Um dies zu verhindern, werden diverse „Prime-and-Boost“Strategien angewandt, bei denen zunächst Plasmid-DNA, die für das entsprechende Transgen 12 1 Einleitung kodiert, appliziert und erst im nächsten Schritt der adenovirale Vektor eingesetzt wird [1, 3, 19, 35, 44]. Seit kurzem existiert eine in Ulm entwickelte neue Technologie zur kombinierten genetischchemischen Modifikation des Kapsids, die sowohl ein Abschirmen der Vektoren als auch eine gezielte Modifikation des Tropismus erlaubt und somit den wesentlichen Problemen gleichzeitig Abhilfe schaffen könnte [15]. Hierbei wurde genetisch ein Cysteinrest in den lösungsmittelzugänglichen HI-Loop des FiberProteins eingeführt. Somit befinden sich insgesamt 36 Cysteine auf der Oberfläche des Vektors, an die unter Bildung von Thioetherbindungen oder Disulfidbrücken kovalent verschiedenartige Liganden gekoppelt werden können. Mit dieser Technologie ist der Tropismus der adenoviralen Vektoren flexibel erweiterbar. Darüberhinaus wurde eine Möglichkeit zur Abschirmung der restlichen Virusoberfläche geschaffen. Durch Kopplung von reaktivem Polyethylenglykol (PEG) an die Aminogruppen der Kapsidoberfläche ergibt sich ein effizientes Polymer-Schild, das sterisch die Bindung an den natürlichen Rezeptor CAR verhindert. Die exponierte Lage der Cysteinreste im HI-Loop erlaubt trotzdem eine Kopplung von Liganden. Hiermit scheint eine echte Spezifizierung des Tropismus und damit eine Erhöhung von Effizienz und Sicherheit der Vektoren möglich (s. Abb. 1.2, S. 15). Das durch die PEGylierung entstandene Schild soll außerdem einen Schutz vor bereits existierenden neutralisierenden Antikörpern darstellen. Besteht keine Immunität, soll die Bildung antiadenoviraler Antikörper verhindert werden. Dadurch würde nicht nur eine erfolgreiche erste Vektorgabe möglich, sondern auch deren Wiederholung. PEG selbst ist nicht immunogen und findet bereits in klinischen Produkten Anwendung. So werden verschiedene Pharmaka (z.B. Filgrastim) an PEG gekoppelt, um ihre Immunogenität zu erniedrigen, die Blutzirkulation und die Bioverfügbarkeit zu verbessern und die Verabreichungshäufigkeit zu reduzieren (www.nektar.com). Es soll in diesem Fall nicht zur Zellfusion (wie beispielsweise in Versuchen zur Erzeugung von Hybridomzellen) dienen, sondern nur zur Abschirmung der Vektorpartikel. Diese wird schon durch eine wesentlich geringere PEG-Konzentration erreicht als sie für eine Zellfusion notwendig ist. 13 1 Einleitung Die im Rahmen dieser Arbeit zu konstruierenden Vektoren sollten auf der Basis dieser Technologie modifizierbar sein. Das sollte weiterführende Versuche beispielsweise zur gerichteten Transduktion von dendritischen Zellen durch Kopplung eines spezifischen Liganden ermöglichen, was nach Abb. 1.1, S. 11 zu einer Präsentation des Transgens auf MHC I- und MHC II-Molekülen und damit einer Aktivierung aller Teile des Immunsystems führen würde. Das könnte sich verstärkend auf die ausgelöste Immunantwort auswirken. 1.4 Das HBsAg als Modellantigen Das Hepatitis B Oberflächenantigen eignet sich gut zur Verwendung als Modellantigen. Mit einem Partikeldurchmesser von 20-30 nm ist es das kleinste der drei Hüllproteine des Hepatitis B Virus. Es besitzt ein konformationelles Epitop, die sog. ‚a’ Determinante, das von den meisten der neutralisierenden Antikörper sowohl im Menschen als auch in Mäusen erkannt wird. Außerdem existieren definierte CTL-restringierte Epitope, wodurch die zelluläre Seite des Immunsystems aktiviert und analysiert werden kann [32, 37]. Von transduzierten Zellen wird das HBsAg sezerniert. International standardisierte Verfahren zur Messung der Immunantwort gegen das HBsAg erleichtern den Vergleich der Ergebnisse von Immunisierungsexperimenten mit denen aus anderen Versuchen. Von Vorteil ist außerdem die Existenz einer Vakzine gegen das Hepatitis B Virus (HBV), die auf diesem Protein basiert und breite Anwendung findet. Dadurch wird der Vergleich zwischen genetischer und rekombinanter protein-basierter Vakzine ermöglicht. 1.5 Das Hepatitis B Virus Das Hepatitis B Virus ist ein umhülltes Virus mit ca. 42 nm im Durchmesser und gehört zur Familie der Hepadnaviridae. Eine Besonderheit ist sein Genom, das aus einer partiell doppelsträngigen DNA (dsDNA) besteht und durch einen komplexen Replikationsmechanismus vervielfältigt wird. Seine Hülle wird im Wesentlichen durch das HBsAg gebildet, 14 1 Einleitung 1. PEGylierung + 20K-NHS-PEG 2. Ligandenkopplung + 3. Kombination von PEGylierung und Ligandenkopplung + Abbildung 1.2 Schematische Darstellung der Technologie zur genetisch-chemischen Kapsidmodifikation adenoviraler Gentransfervektoren Bei der PEGylierung wird reaktives Polyethylenglykol (PEG) (in diesem Fall: N-Hydroxysuccinimid (NHS)-PEG, 20K = 20 Kilodalton) an die Aminogruppen auf der Virusoberfläche gekoppelt. Hierzu sind keine Cysteinreste notwendig. Die Liganden (Lig)-Kopplung wird durch genetisch eingeführte Cysteine (SH) ermöglicht [15], hier beispielhaft über die Maleimidgruppe des Liganden. Abb. modifiziert nach [15] 15 1 Einleitung das nach einer HBV-Infektion in großen Mengen im Blut zu finden ist und gegen das sich ein Großteil der neutralisierenden Antikörper richtet. Daneben existieren noch einige andere Proteine: das Kapsidprotein HBcAg, das nur bei Zerstörung infizierter Zellen durch das Immunsystem im Blut nachgewiesen werden kann und das HBeAg, eine sezernierte Variante des HBcAg [10]. Das Hepatitis B Virus ist verantwortlich für die Hepatitis B, welche parenteral übertragen wird und in verschiedenen Ausprägungen - von subklinisch bis akut - auftreten kann. Ein Übergang in die chronifizierte Form ist möglich und eine Assoziation mit dem hepatozellulären Karzinom wird angenommen. 1.6 Ein Fusionsprotein als Modellantigen Als weiteres Modellantigen wurde ein Fusionsprotein aus Teilen des Ovalbumins, des T-Antigens des Simian Virus 40 (SV40) und aus EGFP gewählt (T-OVA-EGFP). Im Unterschied zu HBsAg verbleibt es nach der Produktion intrazellulär, wo es durch Assoziation des T-Antigen-Teils mit dem Hitzeschockprotein (hsp) 73 stabilisiert wird [18, 27, 31]. Dies führt zu einer verlängerten Halbwertszeit des Proteins und gleichzeitig zur Einschleusung in zusätzliche intrazelluläre Prozessierungswege, wodurch die Präsentation auf MHC I-Molekülen optimiert werden soll. In der Sequenz des T-Antigen-Teils fehlen sowohl die Kernlokalisationssequenz als auch die Bindedomäne für p53. Dadurch besitzt das Protein keine transformierenden Eigenschaften. Die definierte Immunogenität des Ovalbumins erlaubt eine Evaluation der ausgelösten Immunantwort im Vergleich mit anderen Impfmethoden. In diesem Fall ist besonders interessant, wie sich das Verbleiben im Cytosol im Vergleich zur Sekretion des HBsAg auf die Immunantwort auswirkt. Die Fluoreszenz des EGFP sollte die Möglichkeit bieten, die Anzahl der transduzierten Zellen relativ einfach und schnell zu bestimmen und dadurch eventuelle Zusammenhänge zwischen Transduktionseffizienz und Stärke der Immunantwort zu erkennen. 16 2 Zielsetzung 2 Zielsetzung Das Ziel der vorliegenden Arbeit war die Konstruktion und Charakterisierung verschiedener adenoviraler Vektoren, die Modellantigene exprimieren und deren Kapsid mittels der neuen Technologie zur genetisch-chemischen Kapsidmodifikation verändert werden kann. Diese Vektoren sollten es ermöglichen, den Effekt dieser genetisch-chemischen Kapsidmodifikationen auf die Eignung der Vektoren als genetische Vakzine zu untersuchen. Dazu sollten Immunisierungsversuche in vivo dienen. Die Verwendung von zwei verschiedenen Transgenen sollte es zusätzlich erlauben, den Einfluss der Art des Transgens auf die ausgelöste Immunantwort zu evaluieren. Um diese Voraussetzungen zu erfüllen, sollten zwei Erstgenerationsvektoren konstruiert werden, die das Hepatitis B Oberflächenantigen (HBsAg) exprimieren, das von transduzierten Zellen sezerniert wird (AdHBsAg, Ad1CysHBsAg). Zwei weitere sollten die Information zur Expression des Fusionsproteins T-OVA-EGFP beinhalten (AdOVA, Ad1CysOVA). Dieses verbleibt intrazellulär und bietet zudem den Vorteil, dass mit einem Vektor Immunantworten gegen zwei verschiedene Antigene ausgelesen werden können. Jeweils einer der beiden Vektoren sollte die Möglichkeit zur Kapsidmodifikation an genetisch eingeführten Cysteinresten bieten, was später durch ihren direkten Vergleich eine Beurteilung der Modifikationseffekte erlaubt. Zwei Vektoren (mit/ohne Modifikationsmöglichkeit), die nicht für ein Transgen kodieren, sollten zusätzliche Analysen über die Immunreaktion gegen das adenovirale Kapsid zulassen und als Kontrollvektoren dienen (Adempty, Ad1Cysempty). Eine umfassende Charakterisierung mit der Bestimmung der infektiösen und der Gesamtpartikeltiter, der Bestätigung der Transgenexpression und unterschiedlichen Analysen in Bezug auf die Integrität des Vektorgenoms sollte den Konstruktions- und Produktionsvorgang abschließen. 17 2 Zielsetzung In ersten Experimenten in vivo sollte zudem evaluiert werden, ob die konstruierten Vektoren sich zum Auslösen von zellulären und humoralen Immunantworten nach subkutaner bzw. intramuskulärer Injektion eignen. Die zelluläre Immunantwort sollte einerseits mit Hilfe eines Transgen-spezifischen Pentamers und andererseits durch Messung der Interferon-γ- (IFNγ) Produktion restimulierter T-Zellen gemessen werden. Die humorale Antwort sollte mittels ELISA charakterisiert werden. In diesem Sinn sollten die konstruierten Vektoren als Basis für weiterführende, über diese Arbeit hinausgehende Experimente im Bereich der genetischen Vakzinierung dienen. 18 3 Material und Methoden 3 Material und Methoden 3.1 Materialien und Geräte 3.1.1 Materialien Alle verwendeten Chemikalien wurden, sofern im Text nicht anders angegeben, mit dem Reinheitsgrad p.a. von AppliChem (Darmstadt) und Sigma (Taufkirchen) bezogen. Bakterienmedien und –agar wurden in Pulverform bei Invitrogen (Karlsruhe) erworben. Die Enzyme zur DNA-Modifikation stammten von der Firma New England Biolabs (Frankfurt). Zellkulturmedien und Medienzusätze wurden von Invitrogen (Karlsruhe) bezogen. Gefäße für die Zellkultur stammten von der Firma Nunc (Wiesbaden), Eppendorf-Reaktionsgefäße von Eppendorf (Hamburg). Falcon-Röhrchen sowie Rundbodenröhrchen für durchflusszytometrische Messungen wurden bei der Firma Becton-Dickinson (Heidelberg) erworben. 3.1.2 Geräte Die Hersteller und Typen der methodenspezifischen Geräte sind in der Beschreibung der jeweiligen Methode aufgelistet. Darüber hinaus wurden folgende Geräte eingesetzt: ein Autoklav Varioklav (H+P Labortechnik AG, Oberschleißheim), Heizblöcke (HLC, Bovenden), Inkubatoren (Heraeus, Hanau; Memmert, Schwabach), ein pH-Meter MP 225 (Mettler, Toledo), sterile Werkbänke Herasafe (Heraeus, Hanau), die Tischzentrifugen 5417C und 5417R (Eppendorf, Hamburg), Spectrafuge MINI (Neolab, Heidelberg) und Multifuge 3 S-R (Heraeus, Hanau), Wasserbäder (Grant Istruments, Cambridge), ein Ultraschallbad Sonorex (Bandelin, Berlin) sowie Zellkulturinkubatoren mit Isolation und CO2-Begasung BBD 6220 (Heraeus, Hanau). 19 3 Material und Methoden 3.1.3 Verwendete Plasmide Zur Konstruktion der Vektorplasmide (s. Abschnitt 4.1.1, S. 52) wurden die Plasmide pGS66 [30] und pAd1CysPac [16] verwendet. Diese beinhalten jeweils das E1-deletierte Ad5-Genom und zusätzlich bakterielle DNA, basierend auf pBluescript (Stratagene, Heidelberg), die die Amplifikation in Bakterien als Plasmid erlaubt. Das Plasmid pAd1CysPac unterscheidet sich von pGS66 darin, dass es für elf zusätzliche Aminosäuren im Fiber-Protein kodiert, zu denen das für die chemische Kapsidmodifikation notwendige Cystein gehört. 3.1.4 Verwendete Vektoren Für Kontroll- und Vergleichszwecke wurden zusätzlich zu den neu konstruierten auch zwei bereits existierende Vektoren verwendet. Dabei handelte es sich zum einen um den Vektor Ad1stGFP [15], einen Erstgenerationsvektor, der die Expressionskassette des EGFP trägt. Zum anderen wurde der Vektor Ad1Cys [15] verwendet, der durch den zusätzlich eingeführten Cysteinrest die Möglichkeit zur Modifikation bietet und ebenfalls die Expressionskassette des EGFP beinhaltet. 3.1.5 Verwendete Antikörper Die Antikörper Anti-HBsAg-IgG, Anti-T-Ag-IgG, Anti-hsp73-IgG und die Antikörper für die Tierexperimente waren Geschenke von Prof. R. Schirmbeck (Innere Medizin, Ulm). Der AntiEGFP-IgG (Nr. 290) wurde bei Abcam (UK) gekauft und der Sekundärantikörper AntiRabbit-IgG (A-0545 Lot 053K4853) stammte von Sigma, Taufkirchen. 20 3 Material und Methoden 3.1.6 Verwendete Puffer Alle Puffer, die keine hitzelabilen Substanzen enthalten, wurden nach ihrer Herstellung autoklaviert. Die restlichen Puffer (z.B. HEPES) wurden mit einem 0,22 µm Sterilfilter (Schleicher & Schuell, Dassel) sterilfiltriert. 3.2 Arbeiten mit Bakterienkulturen 3.2.1 Flüssigkulturen von E. coli E. coli wurde in Luria Broth Base Medium unter Zusatz von Selektionsantibiotikum kultiviert. Für kleinvolumige Kulturen (2 ml) wurden 2-ml-Eppendorf-Reaktionsgefäße, für großvolumige Kulturen (200 ml) 500-ml-Erlenmeyerkolben verwendet. Als Selektionsantibiotika dienten Ampicillin in einer Endkonzentration von 100 µg/ml oder Kanamycin mit 50 µg/ml. Das Animpfen der Kulturen erfolgte durch Aufnehmen einer einzelnen Kolonie von einer Agarplatte und Überführen in das Medium. Anschließend wurden die Flüssigkulturen bei 250-300 rpm und 37°C in einem Inkubator mit Schüttelvorrichtung (Edmund-BühlerLabortechnik, Hechingen) 12-14 h kultiviert. 3.2.2 Festkulturen von E. coli Zur Selektion einzelner Klone wurden 10-cm-Kulturschalen (Nunc, Wiesbaden), die je 20 ml Luria Broth Agar versetzt mit Selektionsantibiotikum enthielten, verwendet. Die Konzentration der Selektionsantibiotika entsprach der der Flüssigkulturen (s. Abschnitt 3.2.1, S. 21). 21 3 Material und Methoden 3.2.3 Transformation von E. coli Transformation mit Plasmid-DNA Zur Transformation mit Plasmid-DNA wurden zunächst je 40 µl elektrokompetente E. coli (Stamm: XL2-blue, Stratagene, Heidelberg) auf Eis aufgetaut. Nach Zugabe von ca. 100 ng des jeweiligen Plasmides und vorsichtigem Mischen wurde der Ansatz in eine Elektroporationsküvette überführt, die vorher auf Eis gelagert war. Nun folgten die Elektroporation durch Einbringen der Küvette in das Elektroporationsgerät Micropulser (Biorad, München) und das Anlegen einer Spannung von 2,5 kV für ca. 5,7 ms. Anschließend erfolgte eine sofortige Zugabe von 300 µl vorgewärmtem SOC-Medium und der Transfer des gesamten Ansatzes in ein 1,5-ml-Eppendorf-Reaktionsgefäß. Nach Inkubation für 1 h bei 37°C wurden 100 µl auf einer Agarplatte mit entsprechendem Selektionsantibiotikum im Verdünnungsausstrich ausgebracht. Die Agarplatte wurde 12-14 h bei 37°C inkubiert. SOC-Medium (100 ml): 2 g Trypton, 0,5 g Hefeextrakt, 0,05 g NaCl, 1 ml MgSO4 (1 M), 1 ml MgCl2 (1 M), 0,2 ml 20% Glucose Transformation mit DNA aus Ligationsreaktionen Zur Transformation mit DNA aus Ligationsreaktionen (s. Abschnitt 3.3.10, S. 29) wurden jeweils 40 µl elektrokompetente E. coli (Stamm XL2-blue, Stratagene, Heidelberg) auf Eis aufgetaut und mit 1 µl des Ligationsreaktionsgemisches gemischt. Das weitere Vorgehen entsprach dem im vorhergehenden Abschnitt geschilderten. 3.2.4 Plasmidisolierung aus E. coli Plasmidisolierung im kleinen Maßstab Die Plasmidisolierung im kleinen Maßstab wurde eingesetzt, um Plasmide aus Kolonien, die aus der Transformation mit DNA aus 22 3 Material und Methoden Ligationsreaktionen hervorgegangen waren, zu gewinnen (s. Abschnitt 3.2.3, S. 22). Zunächst wurden einzelne Kolonien von den Agarplatten abgenommen, in 2-ml-Flüssigkulturen überführt und 12-14 h bei 37°C im Inkubator mit Schüttelvorrichtung inkubiert (s. Abschnitt 3.2.1, S. 21). Die Kulturen wurden in Tischzentrifugen zentrifugiert (20000g, 1 min, RT), die Mediumüberstände abgesaugt und die Niederschläge in 200 µl TELT-Puffer resuspendiert. Danach wurden die Bakteriensuspensionen 2 min bei 96°C im Heizblock gekocht und anschließend 5 min auf Eis inkubiert. Die Lysate wurden erneut zentrifugiert (20000g, 10 min, RT) und die Überstände in 1,5-ml-Eppendorf-Gefäße transferiert. Nach Mischen mit 100 µl Isopropanol erfolgte erneut eine Zentrifugation (20000g, 10 min, 4°C), um die DNA zu fällen. Die Überstände wurden abgesaugt, die Niederschläge mit 70% Ethanol versetzt und nochmals zentrifugiert (20000g, 10 min, 4°C). Nachdem diese Überstände ebenfalls abgesaugt waren, wurden die Niederschläge bei RT 5-10 min luftgetrocknet und danach in 20 µl TE-Puffer (s. Abschnitt 3.3.1, S. 24) resuspendiert. TELT-Puffer: 50 mM Tris (pH 8,5), 60 mM EDTA, 2,5 M LiCl, 0,4% Triton X-100, 1 Spatelspitze Lysozym Plasmidisolierung im großen Maßstab Die Plasmidisolierung im großen Maßstab wurde eingesetzt, um Plasmide aus Klonen, die aus der Transformation mit Plasmid-DNA hervorgegangen waren, zu gewinnen (s. Abschnitt 3.2.3, S. 22). Einzelne Klone wurden von der Platte abgenommen, in 200-ml-Flüssigkulturen überführt und 12-14 h bei 37°C im Schüttelinkubator inkubiert (s. Abschnitt 3.2.1, S. 21). Die Kulturen wurden in Zentrifugengefäße überführt und zentrifugiert (5000g, 20 min, 4°C, Sorvall RCFC Plus Rotor: SLA-3000). Der Mediumüberstand wurde verworfen. Für die Plasmidisolierung wurden kommerzielle Midiprep-Kits (Qiagen, Hilden) eingesetzt. Die alkalische Lyse und die Reinigung der DNA mittels der mitgelieferten Anionenaustauschersäulen erfolgten gemäß Herstellerangaben. Nach Elution der Plasmid-DNA in 50-ml-Falcon-Röhrchen wurde diese mit 0,7 Volumen Isopropanol versetzt und 1 h bei –20°C inkubiert. Es folgte eine 23 3 Material und Methoden Zentrifugation in einer Zentrifuge mit Ausschwingrotor (4600g, 30 min, 4°C). Der Überstand wurde verworfen, der Niederschlag in 300 µl TE-Puffer resuspendiert und in ein 1,5-mlEppendorf-Reaktionsgefäß überführt. Nun erfolgte eine Ethanolpräzipitation (s. Abschnitt 3.3.3, S. 25). Abschließend wurde der Niederschlag in 200 µl TE-Puffer (s. Abschnitt 3.3.1, S. 24) resuspendiert. 3.3 Arbeiten mit Desoxyribonukleinsäuren 3.3.1 Aufbewahrung von DNA-Lösungen Plasmid-DNA jeglicher Größe sowie DNA-Präparationen aus Virus-Lösungen wurden in TE-Puffer (pH 8,5) bei 4°C gelagert. Vektorfragmente und Insertfragmente für Ligationsreaktionen (s. Abschnitt 3.3.10, S. 29) wurden in 10 mM Tris (pH 7,5) ohne Zusatz von EDTA ebenfalls bei 4°C gelagert. TE-Puffer: 10 mM Tris, 1 mM EDTA, pH 8,5 mit HCl eingestellt 3.3.2 Bestimmung von DNA-Konzentrationen Die Konzentration c von DNA in wässrigen Lösungen wurde mit einem Photometer (Ultrospec 1000, Amersham, Freiburg) bestimmt. Gemäß des Lambert-Beerschen Gesetzes wurde folgender Zusammenhang zur Berechnung der Konzentration aus den gemessenen Extinktionswerten E bei einer Wellenlänge von 260 nm herangezogen: c (dsDNA) [ng/µl] = E260 V 50 V entspricht hierbei dem Verdünnungsfaktor in der Messküvette. 24 3 Material und Methoden 3.3.3 Präzipitation von DNA aus wässrigen Lösungen Ethanolpräzipitation Zur Fällung von DNA aus wässrigen Lösungen wurden diese zunächst mit 0,1 Volumen Natriumacetat (3 M, pH 5,3) und 2,5 Volumen Ethanol (100%) versetzt und gemischt. Anschließend wurde in einer Tischzentrifuge zentrifugiert (20000g, 20 min, 4°C). Der Überstand wurde verworfen, der Niederschlag mit 70% Ethanol gewaschen und nochmals zentrifugiert (20000g, 5-10 min, 4°C). Nach Absaugen des Überstandes wurde der Niederschlag ca. 5-10 min luftgetrocknet und in TE-Puffer (pH 8,5) resuspendiert. Vektor- und Insertfragmente für Ligationsreaktionen (s. Abschnitt 3.3.10, S. 29) wurden in 10 mM Tris (pH 8,5) gelöst. Bei sehr kleinen Mengen und/oder kleinen DNA-Fragmenten wurde der gesamte Ansatz vor der ersten Zentrifugation 1 h bei –20°C inkubiert. Isopropanolpräzipitation Zur Fällung von DNA mit Isopropanol wurden zunächst 0,7 Volumen Isopropanol zugegeben und gründlich gemischt. Anschließend erfolgte eine Zentrifugation (20000g, 5-30 min, 4°C), nach der der Überstand verworfen und der Niederschlag mit 70% Ethanol gewaschen wurde. Nach erneuter Zentrifugation (20000g, 10 min, 4°C) wurde der Überstand abgesaugt, der Niederschlag luftgetrocknet und in TE (pH 8,5) resuspendiert. 3.3.4 Enzymatische Restriktionsanalyse von DNA Für die enzymatische Restriktionsanalyse von DNA mit Restriktionsendonukleasen wurden die vom Hersteller empfohlenen Puffer und Temperaturen verwendet. Die Durchführung bei 37°C erfolgte in einem Inkubator und bei 25°C im Wasserbad. Sollte dieselbe DNA mit zwei verschiedenen Enzymen geschnitten werden, so wurde zwischen den beiden Vorgängen eine Ethanolpräzipitation (s. Abschnitt 3.3.3, S. 25) durchgeführt. 25 3 Material und Methoden Analytische Restriktion Die Standardvolumina für die analytische Restriktion betrugen 10 µl oder 20 µl. Es wurden 5-10 U Enzym/µg DNA verwendet. Meist wurden diese Restriktionsanalysen in Mikrotiterplatten (Nunc, Wiesbaden) durchgeführt. Präparative Restriktion In einem 1,5-ml-Eppendorf-Reaktionsgefäß wurden max. 20 µg DNA in einem Volumen von 100 µl verdaut. Enzymmenge und Restriktionszeit wurden individuell aufeinander abgestimmt, wobei die Herstellerangaben als Richtlinien dienten. Je nach Verwendungszweck wurde der Ansatz anschließend einer Agarosegelelektrophorese (s. Abschnitt 3.3.6, S. 26) mit Gelextraktion (s. Abschnitt 3.3.7, S. 27) oder einer Phenolextraktion (s. Abschnitt 3.3.5, S. 26) unterzogen. 3.3.5 Phenolextraktion von DNA-Lösungen Phenolextraktionen wurden durchgeführt, um Proteine in wässrigen DNA-Lösungen zu inaktivieren und zu entfernen. Dazu wurde das Volumen dieser Lösung mit TE-Puffer (pH 8,5) auf 200 µl aufgefüllt und anschließend mit derselben Menge an TE-äquilibriertem Phenol (Invitrogen, Karlsruhe) versetzt. Es folgten eine Minute kräftiges Mischen, um die Grenzfläche zwischen wässriger und organischer Phase zu vergrößern und eine Zentrifugation (20000g, 5 min, RT). Die wässrige Phase wurde anschließend in ein neues 1,5-ml-EppendorfReaktionsgefäß überführt und mit 200 µl Chloroform-Isoamylalkohol (24:1) versetzt. Erneut wurde eine Minute lang kräftig gemischt und zentrifugiert (20000g, 2-5 min, RT). Nach dem Transfer der wässrigen Phase in ein neues 1,5-ml-Eppendorf-Reaktionsgefäß erfolgte eine Ethanolpräzipitation (s. Abschnitt 3.3.3, S. 25). 3.3.6 Agarosegelelektrophorese von DNA Zur Beurteilung analytischer Restriktionen von DNA (s. Abschnitt 3.3.4, S. 25) oder zur Isolierung von Fragmenten nach präparativen Restriktionen (s. Abschnitt 3.3.4, S. 25) wurde 26 3 Material und Methoden die Agarosegelelektrophorese eingesetzt. Sie erfolgte in horizontalen Elektrophoresekammern (Hoefer, USA) mit 50 ml Gelvolumen und 12 cm Laufstrecke. Als Gel- und Laufpuffer wurden entweder TBE (analytische Gele) oder TAE (präparative Gele) verwendet. Die Agarosekonzentration betrug in Abhängigkeit von der Fragmentgröße sowie der Fragmentgrößendifferenz 0,8-3%. Die Agarose wurde durch Kochen im jeweiligen Puffer gelöst. Nach kurzem Abkühlen wurden 50 µl Ethidiumbromid (c = 0,07%, Applichem, Darmstadt) zugegeben und die Flüssigkeit in die Kammer gegossen. Zur Beladung des Gels wurden die DNA-Proben mit 0,1 Volumen 10-fach Ladepuffer versetzt und in die Geltaschen pipettiert. Die angelegte Spannung betrug 60-100 V. Zur Sichtbarmachung der Fragmente nach der elektrophoretischen Trennung wurde ein UVTransilluminator (Amersham, Freiburg) verwendet, der bei 312 nm die Fluoreszenz des Ethidiumbromids anregt. Für präparative Gele wurde ein DarkReader (Clare Chemical Research, USA) verwendet, um die Bildung von Thymindimeren zu vermeiden. TBE: 90 mM Tris-Borat, 2 mM EDTA, pH 8,0 TAE: 40 mM Tris, 0,1% Eisessig, 1 mM EDTA Ladepuffer (10-fach): 6 mM EDTA, 40% Glycerol, 0,5% Bromphenolblau, 0,5% Xylene cyanole 3.3.7 DNA-Extraktion aus Agarosegelen Die Agarosestücke, die das gewünschte Fragment enthielten, wurden mit Hilfe steriler Skalpelle ausgeschnitten, in maximal 400 mg schwere Portionen geteilt und dann in 2-mlEppendorf-Reaktionsgefäße überführt, wo sie in kleine Stücke zerteilt wurden. Nach Bestimmung des genauen Gewichts wurde 1 µl Phenol/mg Agarose (Invitrogen, Karlsruhe) zugegeben und eine Minute durch kräftiges Schütteln gemischt. Der Ansatz wurde ca. eine 27 3 Material und Methoden Minute in flüssigem Stickstoff eingefroren und danach wieder aufgetaut. Anschließend erfolgte eine Zentrifugation (20000g, 10 min, RT), nach der die wässrige Phase in ein neues Eppendorf-Reaktionsgefäß transferiert wurde. Nach Zugabe der gleichen Menge ChloroformIsoamylalkohol (24:1) wurde erneut kräftig geschüttelt, zentrifugiert (20000g, 5 min, RT) und die wässrige Phase in ein neues Eppendorf-Reaktionsgefäß überführt. Nun wurden 0,1 Volumen Natriumacetat (3 M, pH 5,3) und 0,7 Volumen Isopropanol zugegeben und 30 min bei –20°C inkubiert. Anschließend wurde zentrifugiert (20000g, 10 min, RT) und der Überstand verworfen. Der Niederschlag wurde in 150 µl TE-Puffer (pH 8,5) resuspendiert. Es folgte eine Ethanolfällung (s. Abschnitt 3.3.3, S. 25). 3.3.8 Erzeugung glatter Enden an 5’-Überhängen Glatte Enden an 5’-Überhängen nach präparativer Restriktion wurden mit Hilfe des KlenowEnzyms erzeugt. Dabei wurden dem Ansatz Desoxyribonukleotidtriphosphate (dNTPs) (Endkonzentration je dNTP: 33 µM) und Klenow-Polymerase (1 U/µg DNA) zugegeben. Das Gemisch wurde anschließend genau 20 min bei 30°C im Heizblock inkubiert. Die Reaktion wurde durch Zugabe von Ladepuffer gestoppt und der Ansatz im Agarosegel aufgetrennt, um das gewünschte Fragment anschließend zu extrahieren (s. Abschnitt 3.3.7, S. 27). 3.3.9 Dephosphorylierung des 5’-Endes von DNA-Fragmenten Vor Ligationen wurde bei den Vektorfragmenten (s. Abschnitt 3.3.10, S. 29) eine Dephosphorylierung der 5’-Enden vorgenommen, um eine Selbstligation zu verhindern. Diese Dephosphorylierung erfolgte direkt im Anschluss an die präparative Restriktion (s. Abschnitt 3.3.4, S. 25) durch Zugabe von 5 U alkalischer Kälberdarmphosphatase (CIP) pro 10 µg DNA und Inkubation des gesamten Ansatzes für 45 min bei 37°C. Abschließend wurde eine Phenolextraktion durchgeführt (s. Abschnitt 3.3.5, S. 26). 28 3 Material und Methoden 3.3.10 Ligationen Die Ligationen von DNA erfolgten in einem Gesamtvolumen von 10 µl in 1,5-ml-EppendorfReaktionsgefäßen. Es wurden 400 U T4-DNA-Ligase und der zugehörige Puffer verwendet. Im Folgenden wird das Fragment als Vektorfragment bezeichnet, welches das Resistenzgen trägt; die anderen beteiligten DNA-Stücke heißen Insertfragmente. Vor dem Ansetzen der Ligationsreaktion wurden sowohl Vektor- als auch Insertfragmente 5 min bei 42°C im Heizblock inkubiert, um kohäsive Enden zu trennen und mögliche Supersekundärstrukturen aufzulösen. Pro Ligation wurden 100 ng Vektorfragment und Insertfragment im molaren Verhältnis von 1:3, 1:5 und 1:10 eingesetzt. Diese wurden auf Eis zusammenpipettiert und über Nacht bei Raumtemperatur inkubiert. Als Kontrollen dienten Selbstligationen von Vektor- und Insertfragment. Anschließend erfolgte eine Transformation (s. Abschnitt 3.2.3, S. 22). 3.3.11 DNA-Sequenzierung Die Sequenzierung von Doppelstrang-DNA (dsDNA) erfolgte nach dem Prinzip des „CycleSequencing“ mit der Didesoxymethode und wurde von den „Sequence-Laboratories Göttingen“ als Auftragsarbeit durchgeführt. 3.3.12 Polymerase-Kettenreaktion Durchführung PCR-Reaktionen wurden in einem Gesamtvolumen von 50 µl in 0,5-ml- Eppendorf-Reaktionsgefäßen durchgeführt. Die Nukleotidkonzentration betrug jeweils 200 µM, die jedes Primers 20 pM. Als DNA-Menge wurde bei Plasmid-DNA 1 ng, bei viraler DNA 10 ng gewählt. Es wurden die Taq-DNA-Polymerase (New England Biolabs, Frankfurt) und der mitgelieferte Puffer verwendet. Die gesamte Reaktion erfolgte in einem Thermocycler (Labtech, Burkhardtsdorf). Nach initialer Denaturierung (2 min, 96°C) folgten 30 Zyklen mit 29 3 Material und Methoden Denaturierung (1 min, 96°C), Annealing (1 min, 56°C) und Elongation (1 min, 72°C), die final auf 10 min ausgedehnt wurde. Aufarbeitung von PCR-Reaktionen Die PCR-Reaktionen wurden mit dem „PCR Purification Kit“ (Qiagen, Hilden) gemäß Herstellerangaben gereinigt und anschließend einer Ethanolpräzipitation unterzogen (s. Abschnitt 3.3.3, S. 25). Die ausnahmslos analytischen Reaktionen wurden zur Qualitätskontrolle im Agarosegel analysiert (s. Abschnitt 3.3.6, S. 26) und anschließend zum Sequenzieren geschickt (s. Abschnitt 3.3.11, S. 29). 3.4 Arbeiten mit eukaryotischen Zellen 3.4.1 Zellkulturmedien Als Zellkulturmedien wurden Pulvermedien eingesetzt. Diese wurden nach Herstellerangaben in Wasser gelöst, auf einen pH-Wert von ca. 7,2 eingestellt, steril filtriert und bei 4°C gelagert. Vor Verwendung wurden fötales Kälberserum (FCS) (Endkonzentration 10%) sowie Penicillin-Streptomycin-Glutamin (Endkonzentration 1%) zugesetzt. Für A549-Zellen wurde als Medium MEM verwendet, für N52E6-Zellen α-MEM und für K562-Zellen RPMI 1640. 3.4.2 Kultivierung eukaryotischer Zellen Alle eukaryotischen Zellen wurden bei 37°C und 5% CO2 kultiviert. Sie wurden zweimal pro Woche passagiert, indem sie mit PBS (PAA Laboratories, Pasching) gewaschen und anschließend durch Inkubation mit Trypsin-EDTA-Lösung (1-5 min) (Invitrogen, Karlsruhe) von der Schale abgelöst wurden. Je nach Proliferationsgeschwindigkeit der Zellen wurde ein entsprechendes Aliquot auf neue Kulturschalen überführt und mit frischem Medium aufgefüllt. 30 3 Material und Methoden 3.4.3 Gefrierkulturen eukaryotischer Zellen Zum Einfrieren eukaryotischer Zellen wurden diese zunächst mit PBS (PAA Laboratories, Pasching) gewaschen, dann trypsiniert, anschließend in Medium aufgenommen und in ein Falcon-Röhrchen überführt. Es erfolgte eine Zentrifugation (400g, 10 min, 4°C), der Überstand wurde verworfen und der Zell-Niederschlag in PBS resuspendiert. Nach erneuter Zentrifugation (400g, 10 min, 4°C) wurden die Zellen in der Einfrierlösung resuspendiert und in Portionen zu jeweils 1-2·107 Zellen in Kryoröhrchen (Nunc, Wiesbaden) abgefüllt. Diese wurden in einer Einfrierbox, die mit 100% Isopropanol gefüllt war, mit einer Kühlrate von 1°C/min auf –80°C gekühlt und anschließend in flüssigem Stickstoff gelagert. Zur Reaktivierung wurden diese Zellen in der Hand aufgetaut und in auf 37°C vorgewärmtem Medium resuspendiert. Dann wurden die Zellen zentrifugiert (400g, 10 min, 4°C), der Überstand verworfen und der Zell-Niederschlag in warmem Medium resuspendiert. Nun wurden die Zellen auf Kulturschalen ausplattiert und unter täglichem Mediumwechsel bis zur Konfluenz gezogen. Einfrierlösung: 10% DMSO, 30% FCS, 60% Medium 3.4.4 Transfektion eukaryotischer Zellen Calciumchlorid-Methode Am Vorabend der Transfektion wurden ca. 1-2106 der zu transfizierenden Zellen in 6-cm-Kulturschalen ausgesät. Damit erreicht man in etwa die optimale Zelldichte für Transfektionen. Die Transfektion eukaryotischer Zellen erfolgte mittels Calciumphosphat-DNA-Komplexen, die man folgendermaßen erzeugte: In einem Eppendorf-Reaktionsgefäß wurden 4 µg der für die Transfektion bestimmten DNA mit Wasser auf 176 µl aufgefüllt. Nach anschließender Zugabe von 24 µl 2M CaCl2 und gründlichem Mischen wurde die Lösung unter kräftigem Mischen (Vortex-Genie, Scientific 31 3 Material und Methoden Industries, USA) zu 200 µl HEBS-Puffer (2-fach), der in einem 15-ml-Falcon-Röhrchen vorgelegt war, getropft. Es folgte eine 20-minütige Inkubation des gesamten Ansatzes bei 37°C; währenddessen wurden die Zellen mit PBS gewaschen und das Medium auf 2 ml reduziert. Auf die Zellen wurden anschließend die Calciumphosphat-DNA-Kristalle getropft. Je nach Zelllinie wurde nach 2-12 h Inkubation unter normalen Zellkulturbedingungen das Medium entweder fast vollständig abgesaugt und mit frischem Medium auf 6 ml aufgefüllt oder nur auf 6 ml ergänzt. HEBS-Puffer (2-fach): 50 mM HEPES, 280 mM NaCl, 1,5 mM Na2HPO4, pH 7,13 Superfect-Methode Bei der Transfektion nach der Superfect-Methode wurden am Vorabend ebenfalls 1-2106 Zellen ausgesät. Die Transfektion selbst erfolgte mit Hilfe des Superfect-Transfection-Reagent (Qiagen, Hilden) und wurde nach Herstellerangaben durchgeführt. 3.4.5 Durchflusszytometrie mit eukaryotischen Zellen Die Durchflusszytometrie von eukaryotischen Zellen zum Nachweis der Expression von EGFP (s. Abschnitt 4.3.1, S. 85), CD8 und intrazellulärem IFNγ (s. Abschnitt 3.7.4, S. 48) bzw. der Bindung an spezifische Pentamere (s. Abschnitt 3.7.4, S. 48) erfolgte mit dem Durchflusszytometer FACS-Calibur der Firma Becton-Dickinson (Heidelberg). Im Fall von adhärenten Zellen wurden diese vor der Analyse mit PBS gewaschen und anschließend kurz trypsiniert (100 µl Trypsin/Vertiefung in 24-Loch-Platte). Nach Zugabe von Medium wurden die Zellen durch mehrmaliges Auf-und Abspülen vom Schalenboden gelöst und in ein 2-mlEppendorf-Reaktionsgefäß überführt. Es folgte eine Zentrifugation (400g, 6 min, RT) und anschließendes Resuspendieren des Zellniederschlages in PBS/2% FCS/20 mM EDTA (400 µl für 2105 Zellen). 32 3 Material und Methoden Im Fall von Suspensionszellen wurden diese sofort in ein Eppendorf-Reaktionsgefäß überführt, zentrifugiert und in 400 µl PBS/2% FCS/20 mM EDTA resuspendiert. Nach dem Überführen in FACS-Röhrchen konnten die Zellen analysiert werden. Die Auswertung der Messungen erfolgte mit Hilfe der Software Cell-Quest (Becton-Dickinson, Heidelberg). Die Messungen der murinen Milzzellen erfolgten nach entsprechender Aufbereitung (s. Abschnitt 3.7.3, S. 47). 3.5 Arbeiten mit adenoviralen Vektoren 3.5.1 Verwendete Produktionszelllinien Zur Produktion der Erstgenerationsvektoren wurde die Zelllinie N52E6 [30] verwendet. Diese wurde unter den im Abschnitt 3.4.2, S. 30 erläuterten Bedingungen kultiviert. 3.5.2 Aufbewahrung von adenoviralen Vektoren Gereinigte adenovirale Vektoren wurden in PBS mit 10% Glycerol bei –80°C gelagert. Rohlysate (s. Abschnitt 3.5.5, S. 34) wurden ohne Zusatz von Glycerol ebenfalls bei –80°C gelagert. Vektoren, die zusätzliche Cysteine im Kapsid tragen, wurden zur Vermeidung von Disulfidbrückenbildung in PBS-5 mM Ascorbat-1 mM EDTA (pH 7,1) in Argonatmosphäre gelagert. 3.5.3 Infektion/Transduktion eukaryotischer Zellen mit adenoviralen Vektoren Infektionen bzw. Transduktionen von eukaryotischen Zellen wurden entweder mit gereinigtem Adenovirus oder Virus aus Rohlysaten von Produktionszellen durchgeführt. Die Zellen wurden in reduziertem Medium infiziert und ca. 2 h später auf Normalvolumen 33 3 Material und Methoden aufgefüllt. Die Rohlysate wurden komplett, ohne Entfernung der Zelltrümmer durch Zentrifugieren, verwendet. 3.5.4 Erzeugung von gereinigten Vektoren mit hohem Titer Zur Erzeugung von gereinigten Vektoren mit hohem Titer wurden 10-20 Schalen (Durchmesser 15 cm; 2107 Zellen/Schale) am Vortag gesplitteter N52E6-Zellen mit 10-20 MOI gereinigtem Vektor oder mit durch Titration (s. Abschnitt 3.5.6, S. 35) ermittelter Menge an Rohlysat infiziert. Nach ca. 48 Stunden wurden die Zellen bei vollem zytopathischem Effekt (CPE) geerntet. Der CPE zeigte sich durch abgerundete Zellen, die zu 80% vom Schalenboden abgelöst sind und in Trauben zusammenhängen. Nach der Ernte wurde ein Rohlysat erzeugt (s. Abschnitt 3.5.5, S. 34), das im Dichtegradienten gereinigt wurde (s. Abschnitt 3.5.7, S. 35). 3.5.5 Erzeugung von Rohlysaten aus infizierten Produktionszellen Um Adenoviren aus infizierten Zellen zu gewinnen, wurde zunächst der Mediumüberstand abgenommen und in ein Falcon-Röhrchen überführt. Danach wurden die Zellen entweder mit dem Zellschaber oder durch Abspülen mit der Pipette vom Schalenboden gelöst und ebenfalls in das Gefäß gegeben. Es folgte eine Zentrifugation (400g, 10 min, 4°C), der Überstand wurde verworfen und die Zellen in dem entsprechenden Volumen PBS gelöst. Um die Viren aus den Zellen freizusetzen, wurde das Röhrchen mit den Zellen in flüssigem Stickstoff vollständig eingefroren und anschließend bei 37°C im Wasserbad wieder aufgetaut. Dieser Prozess wurde insgesamt dreimal durchgeführt; das entstandene Lysat wurde entweder zur Infektion neuer Zellen verwendet (s. Abschnitt 3.5.3, S. 33) oder im Dichtegradienten gereinigt (s. Abschnitt 3.5.7, S. 35). Für die abschließende Reinigung der cysteinhaltigen Vektoren im Dichtegradienten wurden diese, statt in PBS, in einem entsprechenden Lysepuffer (s. Abschnitt 3.5.7, S. 35) resuspendiert. 34 3 Material und Methoden 3.5.6 Titration von Rohlysaten Zur Bestimmung der im Rohlysat vorhandenen Virusmenge wurde eine Titration durchgeführt. Dabei wurden am Vortag gesplittete N52E6-Zellen (6 cm-Schale; 1-2106 Zellen) mit unterschiedlichen Mengen des Rohlysates (1 µl, 5 µl, 10 µl, 50 µl, 100 µl) infiziert und nach 48 Stunden auf die Ausprägung des CPE hin untersucht. Durch Hochrechnung auf die entsprechende Zellzahl konnte so die Menge an Rohlysat bestimmt werden, die zur Infektion von Zellen für die Erzeugung gereinigter Vektoren mit hohem Titer (s. Abschnitt 3.5.4, S. 34) benötigt wurde, um nach 48 Stunden eine optimale Ausprägung des CPE zu erhalten. 3.5.7 Dichtegradientenzentrifugation von Rohlysaten Für die abschließende Reinigung von Adenoviren wurde die Zentrifugation in einem CsClDichtegradienten verwendet. Dazu wurde aus den Produktionszellen der letzten Amplifikation (1-2108 Zellen) ein Rohlysat erzeugt (s. Abschnitt 3.5.5, S. 34), das ein weiteres Mal zentrifugiert wurde (3000g, 10 min, 4°C), um die Zelltrümmer zu entfernen. Währenddessen wurden in zwei Ultrazentrifugationsröhrchen (UltraClear, Beckmann, München) CsClLösungen unterschiedlicher Dichte folgendermaßen geschichtet: Zunächst wurden 3 ml einer CsCl-Lösung der Dichte ρ = 1,41 g/ml eingefüllt, darauf wurden vorsichtig 5 ml einer CsClLösung mit ρ = 1,27 g/ml gegeben. Nun wurde der virushaltige Überstand des zentrifugierten Rohlysates abgenommen und zu gleichen Teilen auf die beiden Ultrazentrifugationsröhrchen verteilt, indem er ohne Durchmischen mit den CsCl-Lösungen aufgetragen wurde. Es folgte eine Zentrifugation in der Ultrazentrifuge (Sorvall „Discovery 90SE“, Langenselbold, Ausschwingrotor: Sorvall TH-641)(176000g, 2 h, 4°C). Hiernach wurden die Virusbanden mit einer Injektionsnadel in möglichst geringem Volumen (max. 2 ml) abgezogen und je nach Bandenstärke in ein oder zwei neue Ultrazentrifugationsröhrchen überführt. Diese wurden dann mit einer CsCl-Lösung der Dichte ρ = 1,34 g/ml unter gründlichem Durchmischen mit 35 3 Material und Methoden der Viruslösung aufgefüllt und erneut ultrazentrifugiert (176000g, 20 h, 4°C). Das Abziehen der Banden erfolgte auf gleiche Weise wie nach der ersten Zentrifugation. Vektoren ohne zusätzliche Cysteine: Lyse mit sterilem PBS; Lösung des CsCl ebenfalls in PBS Vektoren, die zusätzliche Cysteine enthalten: Puffer für Lyse und 1. Dichtegradient: 5 mM TCEP, 5 mM EDTA, 5 mM Ascorbat in PBS (pH 7,1, entgast, mit Argon begast) Puffer für 2. Dichtegradient: 2 mM EDTA, 5 mM Ascorbat in PBS (pH 7,1, entgast, mit Argon begast) 3.5.8 Entsalzung der Viren nach Dichtegradientenzentrifugation Unmittelbar nach dem Abziehen der Virusbande aus dem CsCl-Dichtegradienten erfolgte die Entsalzung der virushaltigen Lösung über ein Molekularsieb. Hierzu wurden PD-10-Säulen (Amersham, Freiburg) mit insgesamt 25 ml Elutionspuffer äquilibriert, das Volumen der Virussuspension auf 2,5 ml eingestellt und diese dann auf die Säule aufgetragen. Das Virus wurde anschließend mit 5 ml Elutionspuffer eluiert und in 1-ml-Fraktionen aufgefangen, wobei sich das Virus in den Fraktionen zwei und drei befand, die vereinigt und mit 10% Glycerol versetzt wurden. Dieses Gemisch wurde in 0,5-ml-Portionen aliquotiert und bei –80°C gelagert. Cysteinhaltige Vektoren wurden unter Argonatmosphäre entsalzt und eingefroren. Vektoren ohne zusätzliche Cysteine: Elution mit PBS Vektoren, die zusätzliche Cysteine enthalten: 36 3 Material und Methoden Elutionspuffer: 5 mM Ascorbat, 1 mM EDTA in PBS (pH 7,1, entgast, mit Argon begast) 3.5.9 Präparation von DNA aus gereinigten adenoviralen Vektoren Die Präparation von DNA aus gereinigten Adenoviren erfolgte mit Hilfe des „QiaAmp Mini Kit“ (Qiagen, Hilden). Es wurden 200 µl Virussuspension zu 20 µl der mitgelieferten Proteinase K gegeben. Das weitere Verfahren entsprach den Herstellerangaben. Nach Elution der DNA von der Säule folgte eine Ethanolfällung (s. Abschnitt 3.3.3, S. 25), an deren Abschluss die DNA in 20 µl TE (pH 8,5) resuspendiert wurde. Zur Überprüfung ihrer Integrität wurde diese DNA mit geeigneten Restriktionsenzymen geschnitten (s. Abschnitt 3.3.4, S. 25) und in der Agarosegelelektrophorese analysiert (s. Abschnitt 3.3.6, S. 26). Bei cysteinhaltigen Vektoren diente die präparierte DNA außerdem als Ausgangsmaterial für eine PCR (s. Abschnitt 3.3.12, S. 29) mit anschließender Sequenzierung (s. Abschnitt 3.3.11, S. 29), wodurch das Vorhandensein der Information für die Cysteine bestätigt werden konnte. 3.5.10 Bestimmung des Gesamtpartikeltiters mittels Messung der optischen Dichte Um einen ungefähren Richtwert bezüglich des Titers der gereinigten Virussuspensionen zu erhalten, wurde die optische Dichte bestimmt [21]. Hierzu wurden 158 µl PBS, 2 µl 10% SDS und 40 µl der Virussuspension gemischt, 10 min bei 56°C inkubiert und dann abgekühlt. Als Leerwert diente eine Mischung aus 158 µl PBS, 2 µl 10% SDS und 40 µl 10% Glycerol in PBS, mit der genau gleich verfahren wurde. Bei einer Wellenlänge von 260 nm wurde die optische Dichte gemessen und nach folgender Formel anschließend der Gesamtpartikel-Titer bestimmt: Partikel/µl = OD260·1,1·109·5 37 3 Material und Methoden Bei Vektoren, die zusätzliche Cysteine enthalten, konnte dieses Verfahren aufgrund des ebenfalls bei 260 nm absorbierenden Ascorbates im Puffer nicht angewandt werden. 3.5.11 Slot-Blot zur Bestimmung von Gesamtpartikelzahl und infektiösem Titer Bestimmung des infektiösen Titers Zur Bestimmung des infektiösen Titers einer Virussuspension [14] wurden zunächst A549-Zellen in 24-Loch-Zellkulturschalen in einer Dichte von 1105 Zellen/Vertiefung ausgesät. Am darauffolgenden Nachmittag wurden diese Zellen mit PBS gewaschen und mit 300 µl Medium aufgefüllt. Anschließend erfolgte eine Infektion in Doppelbestimmung mit 2 µl, 10 µl und 20 µl einer Verdünnung des Virus, die sich je nach geschätztem bzw. durch Messung der optischen Dichte bestimmten Titer zwischen 1:10 und 1:50 bewegte. Die Zellen wurden über Nacht bei 37°C und 5% CO2 inkubiert. Danach wurden die Zellen zwei Mal mit 1 ml warmem PBS gewaschen, beim zweiten Mal erfolgte eine 10-minütige Inkubation vor dem Absaugen. Anschließend wurden die Zellen mit 200 µl PBS-50 mM EDTA überschichtet und 20 min bei 37°C inkubiert. Durch Abspülen mit der Pipette wurden sie vom Plattenboden gelöst und in ein 1,5-ml-Eppendorf-Reaktionsgefäß überführt. Zur Erstellung eines Standards wurden 10 Vertiefungen mit nicht-infizierten Zellen genau gleich behandelt und nach Überführung in Eppendorf-Reaktionsgefäße mit geeignetem Plasmidstandard versetzt. Dies 6 erfolgte ebenfalls in Doppelbestimmung über 8 5 Konzentrationsstufen (210 bis 210 Partikelkopien). Nun wurden alle Zellen mit 200 µl 0,8 N NaOH versetzt, kräftig durchmischt und 20-30 min bei RT lysiert. Danach wurden die Proben nochmals kräftig gemischt und jeweils 300 µl (bzw. bei den beiden höchsten StandardProben 338 µl und 375 µl) in die Vertiefungen der Slot-Blot-Apparatur (Hoefer, USA) pipettiert. Mit einer Vakuumpumpe wurden die Lysate auf eine positiv geladene, in 0,4 N NaOH äquilibrierte Nylonmembran (Biodyne Transfer Membran, Pall Corp., Florida) geblottet. Diese wurde anschließend in SSC (2-fach) geschwenkt und 20-30 min bei 120°C in einem Inkubator gebacken. Die Prähybridisierung erfolgte in entsprechendem Puffer 38 3 Material und Methoden (s. Abschnitt 3.5.12, S. 39) bei 68°C für mindestens zwei Stunden. Zur Hybridisierung wurde eine 32P-markierte Sonde verwendet (s. Abschnitt 3.5.12, S. 39). SSC (2-fach): 0,3 M NaCl, 30 mM Natriumcitrat, pH 7,0 Bestimmung der Gesamtpartikelzahl Zur Bestimmung der Gesamtpartikelzahl wurden in einem 1,5-ml-Eppendorf-Reaktionsgefäß zu jeweils 200 µl PBS-50 mM EDTA in Doppelbestimmung 2 µl, 10 µl und 20 µl einer entsprechenden Virusverdünnung gegeben. Die Herstellung des Standards erfolgte auf gleiche Weise unter Verwendung eines geeigneten Standardplasmids, das ebenfalls in Doppelbestimmung und fünf Konzentrationsstufen (s.o.) zu der PBS-EDTA-Lösung pipettiert wurde. Das weitere Vorgehen entsprach dem im vorhergehenden Abschnitt geschilderten. 3.5.12 Detektion immobilisierter Nukleinsäuren auf Nylonmembranen Alle Inkubationen von Nylonmembranen mit Prähybridisierungs-, Hybridisierungs- und Waschlösungen erfolgten in 150-ml-Glasröhren (Wheaton, USA) in einem temperierten Rotationsinkubator (Biometra, Göttingen). Alle Lösungen wurden zuvor in einem Wasserbad temperiert. Prähybridisierung Die Prähybridisierung erfolgte in Prähybridisierungspuffer für ca. 2 h bei 68°C. Prähybridisierungspuffer (20 ml): 2 ml 20-fach SSC, 2 ml 5% Milchpulver, 1 ml Salmon Sperm DNA (300 mg auf 30 ml) 4 ml Dextransulfat (50%), 11 ml destilliertes Wasser 10 min im Wasserbad kochen, auf Eis abkühlen 39 3 Material und Methoden Hybridisierung Im Anschluss an die Prähybridisierung erfolgte die Hybridisierung mit 32 P-markierten DNA-Sonden. Diese wurden kurz vor ihrer Verwendung hergestellt (s.u.) und direkt in den Prähybridisierungspuffer pipettiert. Nach 12-18 h Inkubation bei 68°C im Rotationsinkubator wurde die Nylonmembran zweimal 10 min mit Waschpuffer 1 und einmal 10 und einmal 5 min mit Waschpuffer 2 jeweils bei 68°C gewaschen. Anschließend wurde die Membran in Waschpuffer 2 gelegt, auf Saugpapier luftgetrocknet, in Klarsichtfolie verpackt und in eine Phosphorimagerkassette (Amersham, Freiburg) gelegt. Die Sichtbarmachung der Signale erfolgte einige Stunden später mit Hilfe des Phosphorimagers Storm 860 (Molecular Dynamics, USA) und der Software Image Quant (Molecular Dynamics, USA). Die Titerberechnung erfolgte über die Erstellung einer Geradengleichung für den Plasmidstandard (Microsoft-Excel). Waschpuffer 1: 0,3 M NaCl, 30 mM Natriumcitrat, pH 7,0 0,1 % SDS Waschpuffer 2: 15 mM NaCl, 1,5 mM Natriumcitrat, pH 7,0 0,1 % SDS Herstellung 32P-markierter Sonden Die Herstellung der Sonden erfolgte aus den entsprechenden DNA-Schablonen mittels Klenow-Polymerase und Heptadesoxyribonukleotiden mit zufälliger Sequenz. 200 ng der DNA-Schablone wurden in einem Gesamtvolumen von 45 µl TE (pH 7,5) 5 min gekocht und dann auf Eis abgekühlt. Die Durchführung der Klenow-Reaktion erfolgte mit Hilfe des DNA-Labeling-Kits Rediprime II (Amersham, Freiburg) nach Herstellerangaben unter Zugabe von 32 P-markiertem dCTP (50 µCi). Die im Slot-Blot verwendete Sonde ist das Produkt einer PCR unter Verwendung der beiden Primer fiberseq (ATGAAGCGCGCAAGACCGTCTG) 40 und fiberrev 3 Material und Methoden (CCAGATATTGGAGCCAAACTGCC) und bindet an die Nukleotide 31042-32390 der Ad5-Sequenz. 3.5.13 Bestimmung der Menge des verbliebenen Reduktionsmittels in gereinigten Virussuspensionen Dieser sog. „Ellmann-Test“ wurde durchgeführt, um die Menge des verbliebenen Reduktionsmittels in Lösungen mit gereinigten, cysteinhaltigen Vektoren zu bestimmen. Als Standard wurden sieben Verdünnungen des jeweiligen Reduktionsmittels hergestellt (0,01 mM bis 1 mM). In einer 96-Loch-ELISA-Platte (Nunc, Wiesbaden) wurden dann sowohl von der Viruslösung als auch von jeder Verdünnung der Reduktionsmittel-Lösung 50 µl zu 150 µl einer 1 mM DTNB-Lösung (Ellmann’s Reagenz) gegeben. Die Messung erfolgte in einem ELISA-Reader (VersaMax, Molecular Devices GmbH, München) bei einer Wellenlänge von 412 nm mit der Software SoftmaxPro (Molecular Devices GmbH, München). Durch Erstellen einer Standardgerade ließ sich die Restmenge an Reduktionsmittel in der Viruslösung bestimmen. 3.5.14 Partikelgrößenanalyse durch photonenkorrelierte Spektroskopie Der Polydispersitätsindex der Vorratslösung [15] der cysteinhaltigen Vektorpartikel wurde vermessen, um zu überprüfen, ob während der Produktion der cysteinhaltigen Vektoren eine Aggregatbildung über Disulfidbrücken stattgefunden hat. Die Messung erfolgte in dem Partikelzählgerät Beckman-Coulter N4Plus (Beckman, Krefeld). Dazu wurden 11011 Vektorpartikel mit steril filtriertem, entgastem Wasser auf 3 ml aufgefüllt. Dieses Gemisch wurde in eine Quarzküvette überführt und bei einem Winkel von 90° vermessen (850 s, 20°C). Die Auswertung erfolgte durch die Software PCS Control 2.02. (Beckman, Krefeld). 41 3 Material und Methoden 3.5.15 PEGylierung adenoviraler Vektoren Zur PEGylierung der Vektoren [15] wurde N-Hydroxysuccinimid(NHS)-PEG20K (20 kDa; Nektar Therapeutics, USA) verwendet. Dieses wurde in HEPES-Puffer (50 mM, pH 8,0) gelöst und in 80-fachem Überschuss über Oberflächenaminogruppen zu den ebenfalls in HEPES-Puffer gelösten Vektorpartikeln gegeben. Nach mehrmaligem Mischen wurde 12-14 h bei RT inkubiert und anschließend wurden die Partikel entweder bei –80°C gelagert oder sofort weiterverwendet. 3.6 Arbeiten mit Proteinen 3.6.1 Vorbereitung der Zellen für SDS-PAGE Zur Vorbereitung von Proben aus adhärenten eukaryotischen Zellen wurden diese zweimal mit PBS gewaschen, danach mit PBS-20 mM EDTA überschichtet (1 ml pro 6-cmKulturschale) und 10 min bei 37°C inkubiert. Durch mehrmaliges Auf-und Abspülen wurden die Zellen anschließend vom Schalenboden gelöst, in ein 2-ml-Eppendorf-Reaktionsgefäß überführt und zentrifugiert (400g, 6 min, RT). Nach Absaugen des Überstandes wurden die Zellen in 200 µl Ladepuffer resuspendiert (Vortex-Genie, Scientific Industries, USA) und 10 min bei 96°C in einem Heizblock gekocht. Bei sofortiger Verwendung erfolgte eine Abkühlung auf Eis für 5 min; im Falle der Lagerung wurden die Proben bei –20°C aufbewahrt und vor weiterer Verwendung nochmals für 2-3 min bei 96°C gekocht. Ladepuffer (2-fach): 20% Glycerol (v/v), 0,7 M 2-Mercaptoethanol, 4% SDS (w/v), 125 mM Tris, pH 7,0 1 Spatelspitze Bromphenolblau 42 3 Material und Methoden 3.6.2 SDS-PAGE Zur SDS-Polyacrylamidgelelektrophorese (SDS-PAGE) von Proteinen wurden 10-12% Polyacrylamidgele verwendet, die in Gießapparaturen der Firma Bio-Rad (München) hergestellt wurden. Die Proteinproben (s. Abschnitt 3.6.1, S. 42) wurden nach dem Denaturieren in unterschiedlichen Mengen aufgetragen. Die nachfolgende Elektrophorese erfolgte in mit Laufpuffer gefüllten Kammern der Firma Bio-Rad (München) zunächst bei 60 V. Nach der Passage der Lauffront durch das Sammelgel wurde die Spannung auf 100 V erhöht. Trenngel (10%): 2,5 ml 40% Acryl/Bisacrylamid (29:1), 3,8 ml Tris (1 M pH 8,8), 0,1 ml SDS (10% w/v), 0,1 ml APS (10% w/v), 3,5 ml H2O, 0,004 ml TEMED Sammelgel (3%): 0,38 ml 40% Acryl/Bisacrylamid (29:1), 0,625 ml Tris (1 M pH 6,8), 0,05 ml SDS (10% w/v), 0,05 ml APS (10% w/v), 3,9 ml H2O, 0,005 ml TEMED Laufpuffer (10-fach): 2 M Glycin, 250 mM Tris, 1% SDS (w/v) 3.6.3 Western-Transfer auf Nitrozellulosemembranen Nach der Elektrophorese wurden die Proteine auf Nitrozellulosemembranen (Amersham, Freiburg) transferiert. Hierzu wurde eine Nasstransferapparatur der Firma Bio-Rad (München) eingesetzt. Der Transfer erfolgte in Transferpuffer über 1 h bei 100 V. Transferpuffer: 25 mM Tris, 150 mM Glycin, 20% Methanol (v/v) 43 3 Material und Methoden 3.6.4 Immunologischer Proteinnachweis auf Nitrozellulosemembranen Der Nachweis von Proteinen auf Nitrozellulosemembranen erfolgte mit Hilfe des ECL-Kits (Supersignal West Pico Chemoluminescent Substrate, Pierce, Rockford, IL) und wurde nach Herstellerangaben durchgeführt. Zum Blocken der Membran, was bei 4°C mindestens 1 h lang erfolgte, wurde TBS mit 5% Milchpulver und 0,1% Tween verwendet. Diese Lösung diente auch zum Verdünnen der Antikörper. Sollte der Proteinnachweis nacheinander mit zwei verschiedenen Antikörpern durchgeführt werden, wurde die Membran zwischen den beiden Durchgängen mit 20 ml einer Lösung zur Entfernung der membrangebundenen Antikörper („Stripping“-Puffer) bei 50°C 30 min inkubiert und nach gründlichem Waschen mit TBS erneut mit Milchpulver geblockt. Danach wiederholte sich der Vorgang der Inkubation mit den Antikörpern. TBS: 25 mM Tris, 137 mM NaCl, 27 mM KCl pH 7,4 “Stripping”-Puffer: 60 mM Tris, 2% SDS (w/v), 100 mM 2-Mercaptoethanol 3.6.5 Co-Immunpräzipitation Bei der Co-Immunpräzipitation wurden 5106 Zellen (A549) in einer 10 cm-Schale ausgesät und über Nacht im Brutschrank bei 37°C kultiviert. Am nächsten Tag wurden diese Zellen gewaschen und in reduzierter Mediummenge mit Vektor transduziert. Nach ein bis zwei Stunden wurde das Medium aufgefüllt und für 48 h bei 37°C und 5% CO2 inkubiert. Nach Ablauf dieser Zeit folgten das Waschen der Zellen mit 2 ml PBS, anschließend das Ablösen mit 1 ml Lysepuffer und das Überführen in 2-ml-Eppendorf-Reaktionsgefäße. Zur Lyse wurden diese 30 min schüttelnd auf Eis inkubiert und zentrifugiert (20000g, 30 min, 4°C). Der Überstand wurde in neue Eppendorf-Reaktionsgefäße transferiert, wo er mit 3 µl 44 3 Material und Methoden des zur Präzipitation vorgesehenen Antikörpers (IgG) versetzt wurde. Nach erneuter Inkubation (schüttelnd bei 75 rpm, 60 min, auf Eis) erfolgten die Zugabe von 200 µl ProteinA-Sepharose CL-4B (PAS) (Amersham Biosciences, Uppsala, Schweden), kräftiges Mischen (Vortex) und ein weiterer Inkubationsschritt (schüttelnd bei 150 rpm, 60 min, auf Eis). Der gebildete Protein-Antikörper-PAS-Komplex wurde kurz zentrifugiert (20000g, 15s, RT), der Überstand abgesaugt und anschließend fünf Mal mit 1 ml Waschpuffer gewaschen. Der Waschvorgang wiederholte sich weitere vier Mal, je zwei Mal mit PBS und 0,1 PBS. Zur Trennung von Protein-Antikörper-Komplexen und PAS wurden 300 µl Elutionspuffer zugegeben und kräftig gemischt (Vortex Genie, Scientific Industries, USA). Nach einer Inkubationsphase (schüttelnd, 60 min, 37°C) wurde zentrifugiert (20000g, 30s, RT) und der Überstand in einem neuen Eppendorf-Reaktionsgefäß für 15 min bei –70°C eingefroren. Anschließend wurden die Proben durch ca. fünfstündige Vakuum-Zentrifugation (Centrivac, Heraeus, Hanau) getrocknet und in 40 µl Ladepuffer resuspendiert. Die Proben wurden bei –20°C konserviert, das weitere Vorgehen zur Analyse entsprach dem beim SDS-PAGE und Western Transfer (s. Abschnitte 3.6.2/3.6.3, S. 43) beschriebenen. Lysepuffer: 100 mM Tris/HCl (pH 8,0), 500 mM LiCl, 0,5% NP40, 1% Trasylol, 1 µg/ml Leupeptin Waschpuffer: 100 mM Tris/HCl (pH 8,0), 500 mM LiCl, 0,5% NP40 Elutionspuffer: 5 mM Tris/HCl (pH 6,8), 2% SDS, 5% 2-Mercaptoethanol Ladepuffer (4-fach): 20% Glycerin, 0,7 M 2-Mercaptoethanol, 4% SDS, 0,125 M Tris-HCl (pH 7,0) Bromphenolblau 45 3 Material und Methoden 3.7 Tierexperimentelle Arbeiten Die tierexperimentellen Arbeiten erfolgten zum Großteil in Zusammenarbeit mit Prof. Reinhold Schirmbeck, Infektionsimmunologie, Abteilung Universität Ulm Innere und Medizin wurden I, Sektion nach Molekulare Tierschutzverordnung (Antrag-Nr. 830) durchgeführt. 3.7.1 Immunisierungen Intramuskuläre Immunisierung Die Anästhesie der Mäuse erfolgte mit Hilfe des Inhalationsnarkotikums Isofluran (Forene®, Abbott, Wiesbaden). Anschließend wurde den Mäusen eine bestimmte Dosis des viralen Vektors in einem Volumen von 50 µl beidseits in den Musculus tibialis anterior injiziert. Subkutane Immunisierung Eine bestimmte Vektordosis in PBS in einem Gesamtvolumen von 100 µl wurde den Mäusen ohne Narkose subkutan am Schwanzansatz appliziert. 3.7.2 Antikörpertiterbestimmung im Serum Ca. zwei bis drei Wochen nach der Immunisierung wurde den Mäusen durch Anritzen der Schwanzvene Blut entnommen. Um Serum zu gewinnen, wurde das Blut bis zu seiner Gerinnung bei RT inkubiert und anschließend zentrifugiert (400g, 20 min, RT). Der Überstand wurde abgenommen, in neue Eppendorf-Reaktionsgefäße überführt und bei –20°C gelagert. Antikörper-enzyme-linked immunosorbent assay (ELISA) Zur Bestimmung des Antikörpertiters gegen HBsAg wurde der kommerzielle Test AxSYM IMxAUSAB (Abbott, 46 3 Material und Methoden Wiesbaden), der auf einem kompetitiven ELISA basiert, verwendet. Durch Inkubation HBsAg-konjugierter Mikropartikel mit Mausserum wurde die Bildung von AntigenAntikörper-Komplexen ermöglicht, bei der die beladenen Mikropartikel anschließend irreversibel an eine Glasfasermatrix banden. Hier konnten sie durch Zugabe von biotinyliertem HBsAg, einer anti-Biotin-gekoppelten Phosphatase und deren Substrat sichtbar gemacht werden. Eine Quantifizierung der Antikörper wurde durch die Verwendung von sechs standardisierten Seren ermöglicht; zur Messung war eine Verdünnung der Seren notwendig. Die gemessenen Werte wurden in mIU/ml angegeben. Isotyp-ELISA Die Bestimmung des Isotyps der Antikörper wurde in MicroELISA-Platten (Nunc, Wiesbaden) durchgeführt, wobei sich in den Vertiefungen 150 ng rekombinantes HBsAg und 50 µl Coating-Buffer befanden, die über Nacht bei 4°C inkubiert wurden. Die Platten wurden gewaschen, mit PBS/0,3% BSA geblockt und anschließend wieder gewaschen. Eine Verdünnungsreihe des zu testenden Serums wurde auf die Platten gegeben und 2 h bei RT inkubiert. Es folgte erneutes Waschen und Zugabe von Peroxidase-gekoppelten antiMaus-Isotyp-Antikörpern (Pharmingen, Hamburg) für 1 h. Nach nochmaligem Waschen wurde Substratlösung zugegeben, 15 min später im Dunkeln gestoppt und die Extinktion bei 492 nm und 620 nm gemessen. 3.7.3 Tötung der Mäuse und Aufbereitung der Milzzellen Die Mäuse wurden durch eine Überdosis des Inhalationsnarkotikums Isofluran getötet. Anschließend wurde die Milz für die Bestimmung der T-Lymphozyten entnommen und in 10 ml PBS-1% BSA überführt. Zur Gewinnung einer Einzelzellsuspension wurde die Milz durch ein Stahlgitter gepresst. Anschließend wurden die Zellen zentrifugiert (400g, 10 min, RT) und in warmem Lysepuffer aufgenommen. Nach der Lyse der Erythrozyten wurden die Zellen zweimal gewaschen und anschließend weiterverarbeitet. 47 3 Material und Methoden Lysepuffer (10-fach): 77,0 g NH4Cl, 20,6 g Tris pH 7,2 Waschpuffer: PBS-1% BSA 3.7.4 Nachweis spezifischer zytotoxischer T-Lymphozyten Der Nachweis zytotoxischer T-Zellen wurde auf unterschiedliche Weise durchgeführt. Nachweis Antigen-spezifischer zytotoxischer T-Zellen über Interferon-γ-Produktion nach Restimulation Die Analyse der Milzzellen erfolgte in der Regel in sechsfachem Ansatz in einer 96-Loch-Platte. Es wurden jeweils 1,5105 Zellen in 100 µl Medium (Ultra Culture, Bio Whittaker) mit 1% Penicillin-Streptomycin-L-Glutamin pro Vertiefung verwendet. Zur Stimulation wurde den Zellen 50 ng Antigen-spezifisches Peptid zugesetzt (HBsAg: HBsAg 28-39 IPQSLDSWWTSL, Ovalbumin: OVA_257–264 SIINFEKL, Jerini Bio Tools, Berlin), die Interferon(IFN)-γ-Sekretion wurde anschließend mit 5 µg/ml Brefeldin A inhibiert. Es folgte eine Inkubation (4 h, 37°C), eine Zentrifugation (400g, 4 min, 4°C) und die Vereinigung der sechs Ansätze nach Aufnahme der Zellen in Puffer A. Nach erneuter Zentrifugation (400g, 4 min, 4°C) erfolgte die Zugabe von 1 µg antiCD16/CD32 mAK 2.4G2 und Inkubation (15 min, 4°C), wodurch die Fc-Rezeptoren blockiert wurden, um eine unspezifische Bindung von gegen CD8 gerichteten Antikörpern zu verhindern. Es folgte ein Waschschritt und danach die Färbung der Zellen. Dies geschah durch Inkubation (20-30 min, 4°C) mit einem monoklonalen Antikörper gegen CD8, konjugiert mit R-Phycoerythrin. Nach erneutem Waschen mit Puffer A wurden die Zellen mit 2% Paraformaldehyd in Puffer A fixiert (20 min, RT), gewaschen, in Puffer A resuspendiert und über Nacht bei 4°C gelagert. Am nächsten Tag wurden die Zellen mit Puffer B permeabilisiert (15 min, RT) und zur Detektion des intrazellulären IFNγ mit 48 3 Material und Methoden Fluoroisothiocyanat (FITC)- konjugiertem Antikörper gegen IFNγ (30 min, RT) inkubiert. Nach dreimaliger Wäsche mit Puffer B wurde die Anzahl der CD8-positiven, IFNγ-positiven T-Lymphozyten mit Hilfe eines Durchflusszytometers bestimmt. Puffer A: PBS, 0,5% BSA, 0,1% NaN3 Puffer B: PBS, 0,5% BSA, 0,5% Saponin, 0,05% NaN3 Nachweis positiver T-Lymphozyten unter Verwendung eines Antigen-spezifischen Pentamers Die Milzzellen wurden ebenfalls in einer 96-Loch-Platte analysiert, wobei in jede Vertiefung 1,5106 Zellen gegeben wurden. Nach der Zentrifugation (400g, 4 min, 4°C) wurden 150 µl anti-CD16/CD32 mAK 2.4G2 zugegeben, um eine unspezifische Bindung von anti-CD8-Antikörpern durch Blockierung des Fc-Rezeptors zu verhindern und 15 min bei 4°C inkubiert. Anschließend folgte ein Waschschritt mit Puffer A. Nun wurden 50 µl eines Gemisches aus Antikörpern gegen CD8 (FITC anti-mouse CD8α(Ly), Pharmingen, Hamburg) und dem entsprechenden Pentamer zugegeben und 30 min bei 4°C inkubiert. Nach dreimaligem Waschen mit Puffer A wurden die Zellen in Puffer A in FACS-Röhrchen überführt. Es folgte die Analyse im Durchflusszytometer. 3.7.5 Entnahme transduzierter Gewebe Im Rahmen der Milzentnahme wurden auch die Mm. tibiales anteriores der Mäuse entnommen und in Tissue-Tek (Sakura Finetek, Giessen) eingebettet. Anschließend wurden die Gewebe bei –80°C bis zur weiteren Verarbeitung gelagert. 49 3 Material und Methoden 3.7.6 Immunhistochemischer Nachweis von Transgenen Von dem in Tissue-Tek (Sakura Finetek, Giessen) eingebetteten Gewebe (s. Abschnitt 3.7.5, S. 49) wurden mit einem Kryostat (Leica Microsystems, Nussloch) Schnitte angefertigt und auf mit Silane beschichtete Objektträger überführt. Diese wurden getrocknet und anschließend fünf Minuten in kaltem Aceton fixiert. Es folgten eine 15-minütige Inkubation in Methanol-H2O2 und jeweils 5 Minuten in 70% Isopropanol, 50% Isopropanol und destilliertem Wasser. Nach zweimaligem Waschen in TBS für 30 min wurde mit TBS 0,025% Triton inkubiert, abgesaugt und für 2 h 10% Normalserum entsprechend der Spezies des Zweitantikörpers zugegeben. Nach dem Absaugen wurde über Nacht mit dem ersten Antikörper in entsprechender Verdünnung bei 4°C inkubiert. Drei Spülvorgänge mit TBS von 5 min, 30 min und 1 h gingen der Inkubation mit dem entsprechenden Zweitantikörper voraus. Es folgten mehrmaliges Waschen, 45 min Inkubation mit dem AB-Komplex (Dako, Hamburg) und nach erneutem Waschen die Zugabe von DAB (Sigma, Taufkirchen) für 15 min. Als nächste Schritte folgten Spülen mit destilliertem Wasser, 5 min in Hämalaun und anschließendes Bläuen mit Leitungswasser. Vor dem Eindecken mit Entellan wurde noch eine Alkoholreihe durchlaufen, die 50%, 70%, 96% und absolutes Isopropanol und zum Abschluss Xylol umfasste. Die Präparate wurden anschließend im Lichtmikroskop auf gefärbte Zellen hin untersucht. 3.7.7. Direkter Nachweis der EGFP-Fluoreszenz in Kryoschnitten von Muskelgewebe Zum direkten Nachweis der EGFP-Fluoreszenz in transduziertem Muskelgewebe wurden Kryoschnitte der entnommenen Muskeln angefertigt (s. Abschnitt 3.7.6, S. 50). Anschließend wurden die Schnitte unter einem Fluoreszenzmikroskop (Filter FITC 520 nm) bei Anregung mit 480 nm beurteilt. 50 3 Material und Methoden 3.7.8 Verwendete Statistik Die deskriptive Statistik umfasst die Angabe von Mittelwert und Standardabweichung und wurde mit Hilfe des Programmes Excel (Microsoft) erstellt. Weitergehende vergleichende Berechnungen wurden aufgrund der geringen Fallzahlen nicht durchgeführt. 51 4 Ergebnisse 4 Ergebnisse Es wurden sechs verschiedene adenovirale Gentransfervektoren konstruiert. Zwei von ihnen beinhalten als Transgen das HBsAg (AdHBsAg, Ad1CysHBsAg), zwei weitere kodieren für das Fusionsprotein T-OVA-EGFP (AdOVA, Ad1CysOVA), wobei je ein Vektor dieser beiden Gruppen die Möglichkeit zur späteren chemischen Kapsidmodifikation an Cysteinresten besitzt (Ad1CysHBsAg, Ad1CysOVA). Zwei Vektoren (mit/ohne Modifikationsmöglichkeit), die kein Transgen beinhalten, dienen als Kontrollvektoren (Adempty, Ad1Cysempty). Durch DNA-Klonierung wurden die korrespondierenden infektiösen Plasmide erzeugt, die dazu dienten, die adenoviralen Vektoren zu generieren. Für alle Vektoren wurde der infektiöse und der Gesamtpartikeltiter der Präparation bestimmt und sie wurden durch verschiedene Methoden auf ihre Integrität hin überprüft. Des Weiteren wurden erste in vitro und in vivo Tests mit den Vektoren durchgeführt. Diese sollten Auskunft über die Tauglichkeit der konstruierten Vektoren für weiterführende Experimente zur genetischen Vakzinierung geben. 4.1 Konstruktion und Charakterisierung der Vektoren 4.1.1 Klonierung der Vektoren Die Ausgangsplasmide für die Vektoren, die die Expressionskassette für HBsAg enthalten (pAdHBsAg und pAd1CysHBsAg), wurden folgendermaßen erzeugt: Das Plasmid pCI/Ssmall (Prof. Schirmbeck, Innere Medizin, Ulm) wurde mit den Enzymen ClaI und BglII geschnitten und das kleinere der beiden Fragmente, das die Expressionskassette für HBsAg enthielt (ca. 2,2 kb), isoliert. Nach Auffüllen der Enden mit Klenow wurde dieses Fragment in die ScaI-Schnittstelle der multiplen Klonierungsstelle (MCS) von pGS70 kloniert. Es folgte im zweiten Schritt das Herausschneiden des Fragments mit PacI und die Endklonierung in pGS66 bzw. pAd1CysPac (s. Abschnitt 3.1.3, S. 20). 52 4 Ergebnisse Bei pGS66 handelt es sich um ein sog. „infektiöses Plasmid.“ Es beinhaltet das E1-deletierte Ad5-Genom und zusätzlich bakterielle DNA, die die Amplifikation in Bakterien als Plasmid erlaubt. Diese ist von zwei SwaI-Schnittstellen flankiert, so dass nach dem Schneiden mit diesem Enzym das Virusgenom freigesetzt werden kann. Das Plasmid pAd1CysPac unterscheidet sich von pGS66 nur durch die Information für elf zusätzliche Aminosäuren im Fiber-Protein. Daher konnte für die Vektoren AdHBsAg und Ad1CysHBsAg exakt dieselbe Klonierungsstrategie gewählt werden. Nach Abschluss der Klonierung wurden die Vektorplasmide durch Schneiden mit SwaI linearisiert. Es folgte eine Transfektion (s. Abschnitt 3.4.4, S. 31) in N52E6 und eine anschließende Amplifikation und Reinigung der korrespondierenden Vektoren. Die beiden Vektorplasmide pAdOVA und pAd1CysOVA, die die Expressionskassette für das Fusionsprotein T-OVA-EGFP enthalten, wurden folgendermaßen hergestellt: Das Plasmid pEGFP/cT-OVAkbdb-EGFP (Prof. Schirmbeck, Innere Medizin, Ulm) wurde mit BglII und NotI geschnitten. Das kleinere Fragment, das die Expressionskassette für das Fusionsprotein T-OVA-EGFP enthielt (ca. 2 kb), wurde isoliert und die Enden wurden mit Klenow aufgefüllt. Das Plasmid pCI/Ssmall (s.o.) wurde mit NotI und HindIII geschnitten. Das größere der beiden Fragmente (ca. 4 kb) wurde isoliert und die Enden aufgefüllt. Nun wurde das 2 kb-Fragment aus pEGFP/cT-OVAkbdb-EGFP in das 4 kb-Fragment aus pCI/Ssmall kloniert. Das hieraus entstandene Plasmid pSaV2 wurde mit BglII und ClaI geschnitten. Nach Auffüllen der Enden folgte die Zwischenklonierung in pGS70 und schlussendlich ein Umsetzen in pGS66 und pAd1CysPac (s.o.). Nach Linearisierung mit SwaI erfolgte eine Transfektion in N52E6 und eine anschließende Amplifikation und Reinigung der Vektoren. Abb. 4.1, S. 54 und 4.2, S. 55 zeigen die Klonierungsschemata der Vektoren und Abb. 4.3, S. 56 zeigt die dazugehörigen Vektorkarten. 53 4 Ergebnisse Bgl II pGS70 3,8 kb CMVHBsAgpolyA pCI/Ssmall 4,8 kb Sca I Cla I (1) Pac I ITR ψ Swa I Pac I CMVHBsAgpolyA pSaV 1 6,0 kb Swa I ITR pGS66 / pAd1CysPac 35,8 kb Pac I (2) CMV-HBsAg-polyA ITR ψ Swa I Swa I ITR pAdHBsAg/ pAd1CysHBsAg 38 kb Abbildung 4.1 Klonierungsschema für pAdHBsAg/pAd1CysHBsAg Das BglII/ClaI-Fragment aus pCI/Ssmall, das die Expressionskassette für HBsAg (schwarz) enthält, wurde nach dem Auffüllen der Enden in die ScaI-Schnittstelle von pGS70 kloniert (1). Es entstand als Zwischenstufe pSaV1. Anschließend wurden sowohl dieses Plasmid als auch pGS66 bzw. pAd1CysPac mit PacI geschnitten und die HBsAg-Expressionskassette in das E1-deletierte adenovirale Genom umgesetzt (2). (pAdHBsAg/pAd1CysHBsAg: adenovirale Vektorplasmide, die für das Hepatitis B Oberflächenantigen (HBsAg) kodieren; Cys: zusätzlicher Cysteinrest im Fiber-Protein; pCI/Ssmall: Plasmid, das für HBsAg kodiert; pGS70, pSaV1: Plasmide zur Zwischenklonierung, pGS66/pAd1CysPac: Plasmide, die für das E1-deletierte adenovirale Genom kodieren; E1: Genregion E1 des humanen Adenovirus Serotyp 5; CMV: Cytomegalovirus-Promotor; polyA: Polyadenylierungssignal; ITR: invertierte terminale Sequenzwiederholung; ψ: Verpackungssignal; kb: Kilobasen) 54 4 Ergebnisse CMV CMV Hind III Originalplasmid von T-OVAEGFP 6,1 kb pCI/Ssmall 4,8 kb polyA Bgl II Not I polyA (1) TOVAEGFP Not I Bgl II pSaV 2 5,9 kb CMVT-OVAEGFPpolyA pGS70 3,8 kb Sca I (2) Pac I Cla I ITR ψ Swa I Pac I CMVT-OVAEGFPpolyA pSaV 3 7,0 kb Swa I ITR pGS66 / pAd1CysPac 35,8 kb (3) Pac I CMV-T-OVA-EGFP-polyA ITR ψ Swa I Swa I ITR pAdOVA/ pAd1CysOVA 39,1 kb Abbildung 4.2 Klonierungsschema für pAdOVA/pAd1CysOVA Die Expressionskassette für das Fusionsprotein T-OVA-EGFP (grau) wurde ohne Promotor und polyA durch Schneiden mit BglII und NotI in die HindIII/NotI Schnittstelle von pCI/Ssmall umgesetzt (1). Es entstand die Zwischenstufe pSaV2, die anschließend mit BglII und ClaI geschnitten wurde, um die Expressionskassette, nun durch Promotor und polyA aus pCI/Ssmall vervollständigt, in pGS70 (geschnitten mit ScaI) zu klonieren (2). Aus dem entstandenen pSaV3 wurde abschließend die ganze Expressionskassette mit PacI ausgeschnitten und in die PacI-Schnittstelle von pGS66 bzw. pAd1CysPac umgesetzt (3). (pAdOVA/ pAd1CysOVA: adenovirale Vektorplasmide, die das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimieren; Cys: zusätzlicher Cysteinrest im Fiber-Protein; pCI/Ssmall, pGS70, pSaV2/3: Plasmide zur Zwischenklonierung; pGS66/pAd1CysPac: Plasmide, die für das E1-deletierte adenovirale Genom kodieren; E1: Genregion E1 des humanen Adenovirus Serotyp 5; CMV: Cytomegalovirus-Promotor; polyA: Polyadenylierungssignal; ITR: invertierte terminale Sequenzwiederholung; ψ: Verpackungssignal; kb: Kilobasen) 55 4 Ergebnisse AdHBsAg ITR ψ CMV-HBsAg-polyA ITR Ad1CysHBsAg Cys ITR ψ CMV-HBsAg-polyA ITR fiber AdOVA ITR ψ CMV-T-OVA-EGFP-polyA ITR Ad1CysOVA Cys ITR ψ CMV-T-OVA-EGFP-polyA ITR fiber Abbildung 4.3 Vektorkarten Die Vektoren bestehen von links nach rechts aus dem linken Terminus von Ad5 (bp 1-466, Genbank-Nummer: AY339865.1), der Expressionskassette für das HBsAg (Map-Positionen: 467-2685, BAD44730.1) oder T-OVA-EGFP (Map-Positionen: 467-3734; T-Ag-Fragment (CT272): AS 1-272 mit Deletion von AS 110-152, NP_043127.1; Verbindungspeptid KLRILQSTVP; Ovalbumin-Fragment: AS 246-353, AAB59956; Verbindungspeptid PVAT, EGFP: AAB02572) und dem rechten Terminus von Ad5, wobei in zwei der Vektoren noch ein genetisch eingeführtes zusätzliches Cystein (Cys) im Fiber-Protein enthalten ist. (Ad5: Adenovirus Serotyp 5; AdHBsAg/Ad1CysHBsAg: adenovirale Vektoren, die das Hepatitis B Oberflächenantigen (HBsAg) exprimieren; AdOVA/Ad1CysOVA: Vektoren, die das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimieren; CMV: Cytomegalovirus-Promotor; polyA: Polyadenylierungssignal; ITR: invertierte terminale Sequenzwiederholungen; ψ: Verpackungssignal; bp: Basenpaare; AS: Aminosäure; AS-Abkürzungen: K: Lysin; L: Leucin; R: Arginin; I: Isoleucin; Q: Glutamin; S: Serin; T: Threonin; V: Valin; P: Prolin; A: Alanin ) 56 4 Ergebnisse 4.1.2 Prüfung der Integrität der Vektorgenome Um sicherzustellen, dass während der Amplifikationsschritte kein Rearrangement der Vektorgenome stattgefunden hat, wurde nach der Reinigung der Vektoren zunächst eine Restriktionsanalyse der isolierten Vektor-DNA durchgeführt. Diese erfolgte in allen sechs Fällen mit dem Restriktionsenzym HindIII und wurde anschließend mittels Agarosegelelektrophorese beurteilt. Zum Vergleich wurden die Vektorplasmide aufgetragen, die zuvor außer mit HindIII auch mit SwaI geschnitten worden waren, um die bakteriellen Plasmidelemente vom Virusgenom zu trennen (s. Abb. 4.4, S. 57). Es zeigte sich ein bei Vektor und zugehörigem Plasmid identisches Restriktionsmuster, bei dem alle Plasmide eine p v p v p v p v p v v p v p v p v p v Adempty/ Ad1Cysempty Ad1CysOVA AdOVA Ad1CysHBsAg AdHBsAg Adempty/ Ad1Cysempty Ad1CysOVA AdOVA Ad1CysHBsAg AdHBsAg zusätzliche Bande bei ca. 2900 bp aufwiesen, die dem bakteriellen Segment entspricht. p v v 3054 bp 8000 bp 2036 bp 5090 bp 1636 bp 4072 bp 1018 bp 3054 bp 500 bp Abbildung 4.4 Agarosegelelektrophorese zum Integritätsnachweis der Virus-DNA Nach Schneiden mit HindIII bzw. im Fall der Plasmide mit HindIII und SwaI wurden jeweils 200 ng des Vektorplasmids (p) und der Virus-DNA (v) nebeneinander aufgetragen und im Agarosegel (1%) analysiert. Links und rechts handelt es sich um Aufnahmen desselben Gels zu unterschiedlichen Zeitpunkten (links: oberer Teil des Gels = späte Aufnahme; rechts: unterer Teil = frühe Aufnahme) (AdHBsAg/Ad1CysHBsAg: adenovirale Vektoren, die das Hepatitis B Oberflächenantigen (HBsAg) exprimieren; AdOVA/Ad1CysOVA: adenovirale Vektoren, die das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimieren; Adempty/Ad1Cysempty: adenovirale Vektoren ohne Transgen; Cys: zusätzlicher Cysteinrest im Fiber-Protein; DNA: Desoxyribonukleinsäure; bp: Basenpaare; ng: Nanogramm) 57 4 Ergebnisse 4.1.3 Bestimmung des infektiösen und des Gesamtpartikeltiters Von allen Vektorpräparationen wurde der Titer mittels Slot-Blot (s. Abschnitt 3.5.11, S. 38) bestimmt. Als Hybridisierungssonde wurde eine Sonde gegen einen Teil im Fiber-Protein verwendet (s. Abschnitt 3.5.12, S. 39). Tab. 4.1, S. 58 listet die ermittelten Titer auf. Tabelle 4.1 Gesamtpartikeltiter und infektiöse Titer aller Vektorpräparationen Vektor Gesamtpartikel [vp/µl] infektiöse Partikel [ip/µl] AdHBsAg 4,1108 ± 0,6108 9,3107 ± 1,2107 Ad1CysHBsAg 2,3108 ± 0,2108 4,6107 ± 0,3107 AdOVA 6,2108 ± 0,6108 1,2108 ± 0,3108 Ad1CysOVA n.d. 4,8106 ± 0,3106 Adempty 4,6108 ± 1,1108 1,2108 ± 0,5108 Ad1Cysempty 4,5108 ± 2,0108 2,3108 ± 0,1108 AdHBsAg/Ad1CysHBsAg: adenovirale Vektoren, die das Hepatitis B Oberflächenantigen exprimieren; AdOVA/Ad1CysOVA: adenovirale Vektoren, die das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimieren; Adempty/Ad1Cysempty: adenovirale Vektoren ohne Transgen; Cys: zusätzlicher Cysteinrest im Fiber-Protein; vp: virale Partikel; ip: infektiöse Partikel; n.d: wurde nicht bestimmt; µl: Mikroliter 58 4 Ergebnisse 4.1.4 Überprüfung der Transgenexpression durch Western Transfer Bei allen Vektoren wurde die Expression des entsprechenden Transgens überprüft. Hierzu wurden jeweils 1106 Zellen (A549) ausgesät und mit zwei unterschiedlichen Vektordosen transduziert. Die Probenaufbereitung aus den Zellen erfolgte 48 Stunden später. Als Kontrolle dienten Zellen, die mit 100 MOI des nicht-exprimierenden Vektors Ad1Cysempty transduziert wurden und nicht-transduzierte Zellen. Im Fall der Vektoren AdHBsAg bzw. Ad1CysHBsAg erfolgte der Proteinnachweis mit einem Antikörper gegen das HBsAg (Geschenk von Prof. Schirmbeck, Innere Medizin, Ulm). Abb. 4.5, S. 60 zeigt zwei spezifische Banden bei ca. 25 bzw. 30 kDa nach Transduktion mit AdHBsAg. Nach Transduktion mit Ad1CysHBsAg konnten ebenfalls zwei spezifische Banden detektiert werden (s. Abb. 4.6, S. 61). Diese repräsentieren die nicht-glykosylierte und die glykosylierte Form des HBsAg. Bei Transduktion mit AdOVA bzw. Ad1CysOVA erfolgte die Detektion der Proteine mit zwei verschiedenen Antikörpern. Zunächst wurde ein Antikörper gegen den T-Antigen-Teil des Fusionsproteins eingesetzt (Geschenk von Prof. Schirmbeck, Innere Medizin, Ulm). Nach anschließendem „Strippen“ der Membran (s. Abschnitt 3.6.4, S. 44) erfolgte der Nachweis mit einem Antikörper gegen das EGFP. In beiden Fällen konnte eine Bande bei ca. 75 kDa detektiert werden. Diese Größe entspricht der des gesuchten Fusionsproteins (T-OVA 48 kDa + EGFP 27 kDa) (s. Abb. 4.7, S. 62 und Abb. 4.8, S. 63). 59 4 Ergebnisse AdHBsAg 50 100 K1 K2 50 kDa 37 kDa 25 kDa Abbildung 4.5 Western Transfer zum Nachweis der HBsAg-Synthese in A549-Zellen nach Transduktion mit AdHBsAg Gleiche Volumina jeder Probe wurden in einem 12% Polyacrylamid-Gel analysiert. Die Detektion spezifischer Banden (→) erfolgte mit einem Antikörper gegen HBsAg. (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; 50/100: Transduktion mit 50/100 infektiösen Partikeln von AdHBsAg pro Zelle; K1: transduzierte Kontrolle (Ad1Cysempty); K2: nicht-transduzierte Kontrolle; Ad1Cysempty: cysteinhaltiger adenoviraler Vektor ohne Transgen; A549: humane Lungenkarzinom-Zelllinie; kDa: Kilodalton) 60 4 Ergebnisse Ad1CysHBsAg 50 100 K1 K2 50 kDa 37 kDa 25 kDa Abbildung 4.6 Western Transfer zum Nachweis der HBsAg-Synthese in A549-Zellen nach Transduktion mit Ad1CysHBsAg Gleiche Volumina jeder Probe wurden in einem 12% Polyacrylamid-Gel analysiert. Die Detektion spezifischer Banden (→) erfolgte mit einem Antikörper gegen HBsAg. (Ad1CysHBsAg: cysteinhaltiger adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; 50/100: Transduktion mit 50/100 infektiösen Partikeln von Ad1CysHBsAg pro Zelle; K1: transduzierte Kontrolle (Ad1Cysempty); K2: nicht-transduzierte Kontrolle; Ad1Cysempty: cysteinhaltiger adenoviraler Vektor ohne Transgen; A549: humane Lungenkarzinom-Zelllinie; kDa: Kilodalton) 61 4 Ergebnisse AdOVA 50 100 AdOVA K1 50 K2 100 K1 K2 75 kDa 75 kDa α-T α-GFP Abbildung 4.7 Western Transfer zum Nachweis der Synthese des Fusionsproteins T-OVA-EGFP in A549-Zellen nach Transduktion mit AdOVA Gleiche Volumina jeder Probe wurden in einem 10% Polyacrylamid-Gel analysiert. Zum Nachweis spezifischer Banden (→) wurde ein Antikörper gegen das T-Antigen (α-T) bzw. gegen EGFP (α-EGFP) verwendet. Links und rechts dieselbe Membran vor bzw. nach „Strippen“;. (AdOVA: adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP (T: TAntigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; 50/100: Transduktion mit 50/100 infektiösen Partikeln von AdOVA pro Zelle; K1: transduzierte Kontrolle (Ad1Cysemtpy); K2: nichttransduzierte Kontrolle; Ad1Cysempty: cysteinhaltiger adenoviraler Vektor ohne Transgen; A549: humane Lungenkarzinom-Zelllinie; kDa: Kilodalton; „Strippen“: Entfernung bereits gebundener Antikörper von einer Membran) 62 4 Ergebnisse Ad1CysOVA 50 100 K1 Ad1CysOVA 50 100 K2 K1 K2 75 kDa 75 kDa α-T α-GFP Abbildung 4.8 Western Transfer zum Nachweis der Synthese des Fusionsproteins TOVA-EGFP in A549-Zellen nach Transduktion mit Ad1CysOVA Gleiche Volumina jeder Probe wurden in einem 10% Polyacrylamid-Gel analysiert. Zur Detektion spezifischer Banden (→) wurde ein Antikörper gegen das T-Antigen (α-T) bzw. gegen das EGFP (α-EGFP) verwendet. Links und rechts dieselbe Membran vor bzw. nach „Strippen“ (Ad1CysOVA: cysteinhaltiger adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; 50/100: Transduktion mit 50/100 infektiösen Partikeln von Ad1CysOVA pro Zelle; K1: transduzierte Kontrolle (Ad1Cysempty), K2: nicht-transduzierte Kontrolle; Ad1Cysempty: cysteinhaltiger adenoviraler Vektor ohne Transgen; A549: humane Lungenkarzinom-Zelllinie; kDa: Kilodalton; „Strippen“: Entfernen bereits gebundener Antikörper von einer Membran) 4.1.5 Nachweis der Assoziation von Fusionsprotein und Hitzeschockprotein 73 Die beschriebene intrazelluläre Assoziation des Fusionsproteins T-OVA-EGFP mit dem Hitzeschockprotein kann u.a. zu einer verlängerten Halbwertszeit des Proteins und zu seiner Einschleusung in zusätzliche Prozessierungswege führen. Das könnte sich positiv auf die Immunantwort auswirken und deswegen sollte das Stattfinden der Assoziation auch nach Transduktion mit den entsprechenden Vektoren durch Co-Immunpräzipitation nachgewiesen werden. 5·106 A549-Zellen wurden ausgesät und 24 Stunden später mit jeweils 100 MOI AdOVA bzw. Ad1CysOVA transduziert. Als Kontrolle dienten nicht-transduzierte Zellen. Nach 48 Stunden erfolgte die Ernte der Zellen; die anschließende Co-Immunpräzipitation mit Zelllysat wurde wie in Abschnitt 3.6.5, S. 44 beschrieben durchgeführt. Zur Präzipitation wurde ein Antikörper gegen den T-Antigen-Teil des Fusionsproteins verwendet. In einem Western-Transfer-Experiment wurden die im Präzipitat enthaltenen Proteine analysiert. Zum 63 4 Ergebnisse Nachweis des Fusionsproteins wurde ein Antikörper gegen EGFP eingesetzt. Die Detektion des hsp73, das bei stattgefundener intrazellulärer Assoziation co-präzipitiert werden sollte, erfolgte mit Hilfe eines entsprechenden Antikörpers (Geschenk von Prof. Schirmbeck, Innere Medizin, Ulm). Abb. 4.9, S. 64 zeigt in beiden Fällen eine spezifische Bande bei ca. 75 kDa. Diese entspricht im ersten Fall dem Fusionsprotein (T-OVA 48 kDa + EGFP 27 kDa) und im zweiten Fall dem co-präzipitierten hsp73. Ad Cys Ad K 75 kDa Cys K 75 kDa α-GFP α-hsp73 Abbildung 4.9 Western Transfer zum Nachweis der Assoziation des Fusionsproteins T-OVA-EGFP mit dem Hitzeschockprotein 73 nach Transduktion von A549-Zellen mit 100 infektiösen Partikeln von AdOVA (in der Abbildung: Ad) bzw. Ad1CysOVA (in der Abbildung: Cys) pro Zelle . Die Proteinproben wurden durch Co-Immunpräzipitation des Zelllysats mit einem Antikörper gegen das T-Antigen gewonnen. Gleiche Volumina jeder Probe wurden in einem 10% Polyacrylamid Gel analysiert. Die Detektion der Banden erfolgte mit einem Antikörper gegen EGFP (α-EGFP) bzw. einem Antikörper gegen das Hitzeschockprotein 73 (α-hsp73). Für beide Gele wurde dieselbe Proteinprobe verwendet. (AdOVA/Ad1CysOVA: adenovirale Vektoren, die das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimieren; Cys: zusätzlicher Cysteinrest im Fiber-Protein; K: nicht-transduzierte Kontrolle; A549: humane Lungenkarzinom-Zelllinie; kDa: Kilodalton) 64 4 Ergebnisse 4.1.6 Bestätigung der Existenz der Cysteinreste Die genetisch eingeführten Cysteinreste sind die Voraussetzung für eine spätere chemische Kapsidmodifikation (s. Abb. 1.2, S. 15). Zur Bestätigung ihrer Existenz wurde zunächst der Teil des isolierten Vektorgenoms per PCR amplifiziert (s. Abschnitt 3.3.12, S. 29), der für das Fiber-Protein kodiert und die Information für das zusätzliche Cystein enthalten müsste. Als Primer wurden verwendet: 1. inscheckseq: GAAGGCACAGCCTATACAAACGCTG (bindet an die Nukleotide 32495-32519 der Ad5-Sequenz), 2. inscheckrev: GTTGTGGCCAGACCAGTCCC (bindet an die Nukleotide 32703-32722 der Ad5-Sequenz). Das gereinigte PCR-Produkt wurde im Agarosegel überprüft, wobei ein Größenunterschied von 30-40 bp zwischen dem DNA-Fragment des cysteinhaltigen Vektors Ad1CysHbsAg und dem des zum Vergleich aufgetragenen nicht-cysteinhaltigen Vektorplasmids pAdHBsAg detektiert werden konnte. Da sich durch den Einbau des Cysteins insgesamt elf zusätzliche Aminosäuren im Fiber-Protein befinden, deutet dieser Größenunterschied auf die veränderte Nukleinsäuresequenz, die für das zusätzliche Cystein kodiert, hin. Anschließend wurde das PCR-Produkt sequenziert (s. Abschnitt 3.3.11, S. 29) und mit der Sequenz des Kontrollvektors Ad1Cys (s. Abschnitt 3.1.4, S. 20) verglichen, die das Cystein enthält. Es ergab sich eine vollständige Übereinstimmung (s. Tab. 4.2, S. 67). Der Vektor Ad1Cysempty wurde nicht analysiert, da er aus dem Plasmid pAd1CysPac stammt und dieses wiederum die Grundlage für die Vektoren Ad1CysHBsAg und Ad1CysOVA ist. Da bei diesen beiden Vektoren gezeigt wurde, dass sie das Cystein enthalten, muss deren Ausgangsplasmid (pAd1CysPac) und damit der korrespondierende Vektor Ad1Cysempty zwangsläufig auch das Cystein enthalten. 65 4 Ergebnisse Ad Cys 200 bp Abbildung 4.10 PCR zur Bestätigung der Existenz der Cysteinreste – Analyse der PCR-Produkte in der Gelelektrophorese Ein Teil des Fiber-Proteins von pAdHBsAg (in der Abbildung: Ad) und der isolierten Virus-DNA von Ad1CysHBsAg (in der Abbildung: Cys) wurde per PCR amplifiziert. Die Größe der Amplifikationsprodukte wurde im Agarosegel (3%) überprüft. (PCR: Polymerase-KettenReaktion; pAdHBsAg: adenovirales Vektorplasmid, das für das Hepatitis B Oberflächenantigen (HBsAg) kodiert; Ad1CysHBsAg: cysteinhaltiger adenoviraler Vektor, der das HBsAg exprimiert; bp: Basenpaare) 66 4 Ergebnisse Tabelle 4.2 Sequenzierung der cysteinhaltigen Vektoren zur Überprüfung der Existenz der zusätzlich eingeführten Cysteinreste im Fiber-Protein Vektor Basensequenz (oben)/Aminosäuresequenz (unten) Ad1Cys GGATTAATTGGCGGCGGATGCGGTGGCGGCATCGATGAC G L I G G G C G G G I N N Ad1CysHBsAg GGATTAATTGGCGGCGGATGCGGTGGCGGCATCGATGAC G L I G G G C G G G I N N Ad1CysOVA GGATTAATTGGCGGCGGATGCGGTGGCGGCATCGATGAC G L I G G G C G G G I N N Fett: Insertion im Fiber-Protein (Genbank-Nummer: AAQ19310.1) nach Aminosäure 543 (entspricht dem Nukleotid 32665 in AY339865.1); Ad1Cys: EGFP-exprimierender cysteinhaltiger Vektor, dessen Sequenz hier zum Vergleich dient; Ad1CysHBsAg: cysteinhaltiger adenoviraler Vektor, der das Hepatitis B Oberflächenantigen exprimiert; Ad1CysOVA: cysteinhaltiger adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; Basenabkürzungen: G: Guanin, A: Adenin; T: Thymin; C: Cytosin; Aminosäureabkürzungen: G: Glycin, L: Leucin, I: Isoleucin, C: Cystein, N: Asparagin 67 4 Ergebnisse 4.1.7 Messung des Polydispersitätsindex Von den gereinigten Virussuspensionen der cysteinhaltigen Vektoren wurde der Polydispersitätsindex bestimmt. Dieser gibt Auskunft über die Größenverteilung der Partikel in einer Suspension und dient so der Qualitätskontrolle einer Viruspräparation, da sich auf diese Weise eine eventuelle Aggregatbildung durch Disulfidbrückenbindungen während der Vektorreinigung erkennen lässt. Diese Messung erfolgte wie in Abschnitt 3.5.14, S. 41 beschrieben und ergab die in Tab. 4.3, S. 68 enthaltenen Werte. Abb. 4.11, S. 69 zeigt exemplarisch das Messergebnis von Ad1CysOVA. Tabelle 4.3 Polydispersitätsindices der gereinigten Virussuspensionen Vektor Polydispersitätsindex Ad1CysHBsAg 0,161 ± 0,022 Ad1CysOVA 0,067 ± 0,022 Ad1Cysempty n.d. Ad1CysHBsAg: cysteinhaltiger adenoviraler Vektor, der das Hepatitis B Oberflächenantigen exprimiert; Ad1CysOVA: cysteinhaltiger adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; Ad1Cysempty: cysteinhaltiger adenoviraler Vektor ohne Transgen; n.d: wurde nicht bestimmt 68 4 Ergebnisse Abbildung 4.11 Messung des Polydispersitätsindex der gereinigten Virussuspension von Ad1CysOVA (exemplarisch) (Ad1CysOVA: cysteinhaltiger adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert) 69 4 Ergebnisse 4.1.8 Bestimmung des Reduktionsmittelgehaltes der gereinigten Virussuspensionen Der Ellmann-Test ist ebenfalls eine Methode der Qualitätskontrolle von Vorratslösungen der cysteinhaltigen Vektoren. Er wurde durchgeführt, um die Menge des verbliebenen Reduktionsmittels in den gereinigten Virussuspensionen zu bestimmen. Der Grund hierfür ist, dass das Reduktionsmittel Einfluss auf die Integrität von redoxsensitiven Liganden (z.B. Transferrin) hat. Tab. 4.4, S. 70 zeigt die Ergebnisse der Messungen. Tabelle 4.4 Reduktionsmittelgehalt der gereinigten Virussuspensionen Vektor Reduktionsmittel [µM] Ad1CysHBsAg 3,4 Ad1CysOVA n.d. Ad1Cysempty 1,7 Ad1CysHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen exprimiert; Ad1CysOVA: adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; Ad1Cysempty: adenoviraler Vektor ohne Transgen; Cys: zusätzlicher Cysteinrest im Fiber-Protein; n.d: wurde nicht bestimmt; µM: Mikromol 70 4 Ergebnisse 4.2 Immunisierungsversuche mit AdHBsAg und AdOVA 4.2.1 Immunisierung mit AdHBsAg zur Dosis- und Injektionsroutenfindung Die Vektoren sollten nun im Hinblick darauf geprüft werden, ob sie in vivo zelluläre und humorale Immunantworten auslösen können. Hierzu wurden steigende Vektordosen von AdHBsAg in BALB/cAnNCrl (BALB/c)-Mäuse injiziert. Parallel wurden zwei unterschiedliche Injektionsrouten, subkutan (s.c.) und intramuskulär in den Musculus tibialis anterior (i.m.), getestet. Um die ausgelöste Immunantwort quantitativ einordnen zu können, erhielt eine Vergleichsgruppe von Mäusen 50 µg Plasmid-DNA mit identischer Expressionskassette für HBsAg. Diese Menge entspricht dem Standard bei genetischer Vakzinierung mit Plasmiden. Tab. 4.5, S. 71 zeigt den Injektionsplan. In einem weiteren Schritt wurde ein Boost-Experiment durchgeführt, indem einigen Mäusen dieselbe Vektordosis zu einem späteren Zeitpunkt erneut injiziert wurde. Eine eventuelle positive Auswirkung auf die Quantität der Immunantwort sollte anschließend evaluiert werden. Tabelle 4.5 Injektionsplan zur Findung von geeigneter Dosis und Injektionsroute Lfd. Anzahl Nr. Mäuse Vektor/ Plasmid Vektordosis o. Plasmidmenge/Seite Injektionsroute Applikationsvolumen [µl] 1 5 AdHBsAg 1108 vp i.m. 50 2 5 AdHBsAg 1109 vp i.m. 50 3 3 AdHBsAg 11010 vp i.m. 50 4 5 AdHBsAg 1108 vp s.c. 100 5 5 AdHBsAg 1109 vp s.c. 100 6 5 pCI/Ssmall 50 µg i.m. 50 AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; pCI/Ssmall: Plasmid, das für HBsAg kodiert; vp: virale Partikel; s.c: subkutan; i.m: intramuskulär; µ: Mikro- 71 4 Ergebnisse Analyse der zellulären Immunantwort im Pentamer- und im Interferon-γ-Assay Zur Analyse der zellulären Immunantwort wurden jeweils zwei Mäuse einer Gruppe (ausgenommen Gruppe 3) nach 14 Tagen getötet. Nach Entnahme der Milz wurden die Splenozyten aufbereitet (s. Abschnitt 3.7.3, S. 47) und sowohl im Pentamer- als auch im IFNγAssay analysiert. Der Pentamer-Assay (s. Abschnitt 3.7.4, S. 48) wurde mit einem Antikörper gegen CD8 und dem Pentamer „Ld/S“ (H-2Ld MHC Pro5TM pentamer peptide: IPQSLDSWWTSL, ProImmune Limited, Oxford, UK) durchgeführt, das die Präsentation von HBsAg-Peptiden auf einem MHC I-Komplex simuliert. Die Anzahl der doppelt- (CD8+Ld/S+) positiven Zellen wurde in der Durchflusszytometrie gemessen (s. Abb. 4.12, S. 73). Im anschließenden Vergleich der T-Zell-Antworten der verschiedenen Gruppen ergab sich Folgendes: Die Mäuse, die mit viralen Vektoren immunisiert worden waren, bildeten in der Tendenz eine deutlich höhere, je nach Dosis drei- bis siebenfache, Immunantwort als die Plasmid-immunisierten Mäuse. Zusätzlich deuteten die gemessenen Werte auf eine positive Korrelation zwischen injizierter Vektordosis und T-Zell-Anzahl hin. Dies ließ sich sowohl bei intramuskulärer als auch bei subkutaner Injektionsroute beobachten. Zwischen den beiden gewählten Routen war kein wesentlicher Unterschied zu erkennen. Als Negativkontrolle diente die Milz einer nicht-immunisierten Maus, für die sich der Wert 0,1% für die doppeltpositiven Zellen ergab. Im IFNγ-Assay (s. Abschnitt 3.7.4, S. 48) wurden die Milzzellen mit einem Peptid des HBsAg stimuliert; anschließend erfolgte eine intrazelluläre Anfärbung des produzierten Interferons. Die Anzahl der sowohl CD8- als auch IFNγ-positiven Zellen wurde im Durchflusszytometer gemessen. Es ergaben sich ebenfalls deutliche Hinweise dafür, dass mit viralen Vektoren höhere zelluläre Immunantworten erreicht werden können als mit Plasmid-DNA. Auch die Dosisabhängigkeit der Anzahl positiver T-Zellen deutete sich an. Als Negativkontrolle diente eine nicht-immunisierte Maus, bei der sich für doppelt-positive Zellen der Wert 0,00% ergab. Die Ergebnisse sind in Abb. 4.13, S. 74 dargestellt. 72 4 Ergebnisse A i.m. AdHBsAg 1108 vp s.c. AdHBsAg 1109 vp AdHBsAg 1108 vp AdHBsAg 1109 vp Plasmid 50 µg 4.0% 1.5% 2.1% 0.5% 1.1% 2.7% 1.0% 1.1% 0.4% CD8+ 2.7% Ld/S pentamer+ B 4,5 4 + % CD8 Ld/S + 3,5 3 2,5 2 1,5 1 0,5 0 1E+08 vp 1E+09 vp 1E+08 vp 1E+09 vp (n=2) (n=2) (n=2) (n=2) i.m. s.c. Plasmid 50µg i.m. (n=2) Abbildung 4.12 Pentamer-Assay nach Immunisierung mit AdHBsAg zur Dosis- und Injektionsroutenfindung An Tag 14 nach der Vektorinjektion wurde jeweils zwei Mäusen der Gruppen 1, 2, 4, 5 und 6 (s. Tabelle 4.5, S. 71) die Milz entnommen. Nach Durchführung des Pentamer-Assays wurde mit Hilfe der fluoreszenzgestützten durchflusszytometrischen Analyse der Splenozyten die Zahl HBsAg-spezifischer zytotoxischer T-Zellen (Ld/S+CD8+) ermittelt. Die Angaben in Prozent beziehen sich jeweils auf die Gesamtheit der CD8-positiven (CD8+) Zellen und stellen die Mittelwerte der einzelnen Gruppen dar. Für die nicht-immunisierte Kontrolle ergab sich der Wert 0,1% für doppelt-positive Zellen. (A) Originaldaten (zwei Mäuse einer Gruppe untereinander dargestellt) (B) Zusammenfassung der Ergebnisse im Balkendiagramm (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; Plasmid: für HBsAg kodierendes Plasmid; Ld/S+: positiv für das Pentamer Ld/S; CD: Differenzierungsmarker; i.m: intramuskulär; s.c: sub-kutan; n: Anzahl der Tiere; vp: virale Partikel; µg: Mikrogramm) 73 4 Ergebnisse 1,4 1,2 % CD8 IFN + + 1 0,8 0,6 0,4 0,2 0 1E+08 vp 1E+09 vp (n=2) (n=2) 1E+08 vp 1E+09 vp (n=2) (n=2) i.m. Plasmid 50µg i.m. (n=2) s.c. Abbildung 4.13 IFNγ-Assay nach Immunisierung mit AdHBsAg zur Dosis- und Injektionsroutenfindung An Tag 14 nach der Vektorinjektion wurde jeweils zwei Mäusen der Gruppen 1, 2, 4, 5 und 6 (s. Tabelle 4.5, S. 71) die Milz entnommen. Nach Durchführung des IFNγAssays wurde mittels durchflusszytometrischer Analyse der Splenozyten die Zahl HBsAg-spezifischer zytotoxischer (IFNγ+CD8+) TLymphozyten ermittelt. Die Angaben in Prozent beziehen sich jeweils auf die Gesamtheit der CD8-positiven (CD8+) Zellen und stellen die Mittelwerte der einzelnen Gruppen dar. Für die nicht-immunisierte Kontrolle ergab sich ein Wert von 0,00% doppelt-positiver Zellen. (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; Plasmid: für HBsAg kodierendes Plasmid; IFNγ+: Interferon-γ-positiv; CD: Differenzierungsmarker; i.m: intramuskulär; s.c: subkutan; n: Anzahl der Tiere; vp: virale Partikel; µg: Mikrogramm) Analyse der humoralen Immunantwort im ELISA An Tag 29 wurde den verbliebenen drei Mäusen jeder Gruppe Blut aus der Schwanzvene entnommen und der Titer der gegen HBsAg gerichteten Antikörper bestimmt. Dies erfolgte mit Hilfe des in Abschnitt 3.7.2, S. 46 beschriebenen ELISA. In der Auswertung ergaben sich Anhaltspunkte für eine Abhängigkeit des Antikörpertiters von der applizierten Vektordosis. Im Fall der Plasmid-immunisierten Mäuse zeigte sich eine Tendenz zu höheren Antikörper-Werten als bei den Mäusen, die mit viralen Vektoren immunisiert worden waren. Die Ergebnisse von intramuskulärer bzw. subkutaner Injektion waren gleichwertig. Die Isotypisierung der Antikörper ergab überwiegend IgG 2a. Die Ergebnisse sind in Abb. 4.14, S. 75 dargestellt. 74 Spezifische Antikörper (mIU/ml) 4 Ergebnisse 4000 3500 3000 2500 2000 1500 1000 500 0 1E+08 vp 1E+09 vp 1E+10 vp 1E+08 vp 1E+09 vp Plasmid (n=3) (n=3) (n=3) (n=3) (n=2) 50 µg i.m. (n=3) i.m. s.c. Abbildung 4.14 Antikörper-ELISA nach Immunisierung mit AdHBsAg zur Dosis- und Injektionsroutenfindung An Tag 29 nach der Vektorinjektion wurde zwei bzw. drei Mäusen der Gruppen 1-6 (s. Tabelle 4.5, S. 71) Blut entnommen und mittels ELISA auf HBsAgspezifische Antikörper untersucht. Dargestellt sind die Mittelwerte der einzelnen Gruppen. (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; Plasmid: für HBsAg kodierendes Plasmid; ELISA: enzyme-linked immunosorbent assay; i.m: intramuskulär; s.c: subkutan; n: Anzahl der Tiere; vp: virale Partikel; µg: Mikrogramm; mIU: 10-3 internationale Einheiten) Ergebnisse des Boost-Experiments Zur Evaluation der Auswirkungen einer zweiten Immunisierung mit gleicher Dosis innerhalb von vier bis sechs Wochen nach der ersten Injektion („Boost“) wurde den verbliebenen drei Mäusen der Gruppen 2 (1108 vp, i.m.) und 5 (1108 vp, s.c.) (s. Tab. 4.5, S. 71) an Tag 36 dieselbe Vektormenge unter gleichen Bedingungen (Injektionsvolumen und -route) erneut injiziert. Nach weiteren 13 Tagen erfolgte eine Blutentnahme und nach Tötung der Mäuse die Entnahme und Analyse der Milzzellen. Die Anzahl spezifischer T-Lymphozyten wurde mit dem Pentamer-Assay bestimmt. Im Vergleich zur ersten Immunisierung deutete sich eine Steigerung der Anzahl doppeltpositiver T-Zellen um das ca. Eineinhalb (i.m.)- bis Vierfache (s.c.) an (s. Abb. 4.15, S. 76). Der Antikörpertiter war sowohl bei intramuskulärer als auch bei subkutaner Applikation im 75 4 Ergebnisse Vergleich zu den Werten vor dem Boost erhöht. Abb. 4.16, S. 77 fasst die Ergebnisse zusammen. 8 7 + % CD8 Ld/S + 6 5 vor Boost 4 nach Boost 3 2 1 0 1E+08 vp i.m. (n=3) 1E+08 vp s.c. (n=3) Abbildung 4.15 Pentamer-Assay zur Auswertung des AdHBsAgBoost-Experiments Drei Mäusen der Gruppen 2 und 5 (s. Tabelle 4.5, S. 71) wurde an Tag 36 nach der ersten Immunisierung dieselbe Vektordosis unter gleichen Bedingungen erneut injiziert. An Tag 49 wurden ihre Milzen entnommen, der Pentamer-Assay durchgeführt und die Anzahl der HBsAgspezifischen zytotoxischen (Ld/S+CD8+) T-Zellen durchflusszytometrisch gemessen. Die Angaben in Prozent beziehen sich jeweils auf die Gesamtheit der CD8-positiven (CD8+) Zellen und stellen die Mittelwerte der einzelnen Gruppen dar. Dargestellt ist ein Vergleich der Werte vor dem Boost (Tag 14, schwarz) und nach dem Boost (Tag 49, gestreift). Für nichtimmunisierte Kontrollmäuse ergab sich der Wert 0,05% für doppeltpositive Zellen. (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; Ld/S+: positiv für das Pentamer Ld/S; CD: Differenzierungsmarker; i.m: intramuskulär; s.c: subkutan; n: Anzahl der Tiere; vp: virale Partikel) 76 4 Ergebnisse spezifische Antikörper (mIU/ml) 2500 2000 1500 vor Boost nach Boost 1000 500 0 1E+08 vp i.m. 1E+08 vp s.c. (n=3) (n=2) Abbildung 4.16 Antikörper-ELISA zur Auswertung des AdHBsAgBoost-Experiments An Tag 36 nach der ersten Immunisierung wurde drei Mäusen der Gruppen 2 und 5 (s. Tabelle 4.5, S. 71) dieselbe Vektordosis unter gleichen Bedingungen erneut injiziert. An Tag 49 wurde den Mäusen Blut entnommen und mittels ELISA auf HBsAg-spezifische Antikörper untersucht. Dargestellt sind jeweils die Mittelwerte der Gruppen zum Vergleich der Antikörpertiter vor dem Boost (Tag 29, schwarz) und nach dem Boost (Tag 49, gestreift). (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; ELISA: enzymelinked immunosorbent assay; i.m: intramuskulär; s.c: subkutan; n: Anzahl der Tiere; vp: virale Partikel; mIU: 10-3 internationale Einheiten) 4.2.2 Versuche zur Ausweitung des Dosisbereichs mit AdHBsAg und zur Bestimmung einer Schwellendosis Die generierten Vektoren erlauben chemische Kapsidmodifikationen, die die Möglichkeit zu spezifisch gerichtetem Gentransfer bieten, u.a. mit dem Ziel, unter Verwendung möglichst geringer Vektordosen eine bestmögliche Immunantwort zu erzielen. Um also das Potential dieser Technologie evaluieren zu können, sollte bekannt sein, in welchem Dosisbereich man sich mit nicht-modifizierten Vektoren bewegen kann und ob es möglicherweise eine Schwelle 77 4 Ergebnisse gibt, unter der keine Immunantwort mehr auslösbar ist. Da vor allem der niedrige Dosisbereich von Interesse ist, wurden drei weitere Gruppen von Mäusen (Stamm: BALB/c) mit Vektordosen von 1106, 1107 und 1108 vp immunisiert. Tab. 4.6, S. 78 zeigt den Injektionsplan. Tabelle 4.6 Injektionsplan für die Ausweitung des Dosisbereichs und die Bestimmung einer Schwellendosis Lfd. Anzahl Nr. Mäuse Vektor/ Plasmid Vektordosis o. Plasmidmenge/Seite Injektionsroute Applikationsvolumen [µl] 1 4 AdHBsAg 1106 vp i.m. 50 2 4 AdHBsAg 1107 vp i.m. 50 3 4 AdHBsAg 1108 vp i.m. 50 AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen exprimiert; i.m: intramuskulär; vp: virale Partikel; µl: Mikroliter Analyse der zellulären Immunantwort im Pentamer- und im IFNγ-Assay An Tag 13 nach der Immunisierung wurden zwei Mäuse aus jeder Gruppe getötet, die Milz entnommen und die T-Zell-Antwort untersucht. Es wurde sowohl der Pentamer- als auch der IFNγ-Assay mit anschließender durchflusszytometrischer Messung durchgeführt. Mit beiden Methoden waren bei der Dosis von 1106 Vektorpartikeln kaum spezifische T-Lymphozyten detektierbar, während bei 1107 Partikeln ein deutlicher Anstieg sichtbar war. Für die nicht-immunisierten Mäuse ergaben sich Werte von 0,00% doppelt-positiver Zellen im IFNγ- und 0,15% im Pentamer-Assay. Abb. 4.17, S. 79 zeigt die Ergebnisse der Analyse im Pentamer-Assay, Abb. 4.18, S. 80 zeigt die aus dem IFNγ-Assay. 78 4 Ergebnisse Analyse der humoralen Immunantwort An Tag 36 wurde den verbliebenen zwei Mäusen Blut entnommen. Mittels ELISA wurde der Antikörpertiter gegen HBsAg bestimmt. Hierbei konnten unterhalb einer Dosis von 1108 Vektorpartikeln keine spezifischen Antikörper gemessen werden. Die Ergebnisse zeigt Abb. 4.19, S. 81. 9 8 + % CD8 Ld/S + 7 6 5 4 3 2 1 0 1E+06 vp (n=2) 1E+07 vp (n=2) 1E+08 vp (n=2) Abbildung 4.17 Pentamer-Assay nach intramuskulärer Immunisierung mit AdHBsAg zur Ausweitung des Dosisbereichs An Tag 13 nach der Vektorinjektion wurde jeweils zwei Mäusen der Gruppen 1-3 (s. Tabelle 4.6, S. 78) die Milz entnommen. Die Splenozyten wurden im Pentamer-Assay aufbereitet; anschließend wurde durchflusszytometrisch die Anzahl HBsAg-spezifischer zytotoxischer (Ld/S+CD8+) TLymphozyten bestimmt. Die Angaben in Prozent beziehen sich jeweils auf die Gesamtheit der CD8-positiven (CD8+) T-Zellen und stellen die Mittelwerte der einzelnen Gruppen dar. Für die nicht-immunisierte Kontrolle ergab sich der Wert 0,15% für doppelt-positive T-Zellen. (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; Ld/S+: positiv für das Pentamer Ld/S; CD: Differenzierungsmarker; n: Anzahl der Tiere; vp: virale Partikel) 79 4 Ergebnisse 1,2 1 % CD8 IFN + + 0,8 0,6 0,4 0,2 0 1E+06 vp (n=2) 1E+07 vp (n=2) 1E+08 vp (n=2) Abbildung 4.18 IFNγ-Assay nach intramuskulärer Immunisierung mit AdHBsAg zur Ausweitung des Dosisbereichs An Tag 13 nach der Vektorinjektion wurde jeweils zwei Mäusen der Gruppen 1-3 (s. Tabelle 4.6, S. 78) die Milz entnommen. Nach Durchführung des IFNγ-Assays wurden die Splenozyten durchflusszytometrisch analysiert und die Anzahl der HBsAg-spezifischen zytotoxischen (IFNγ+CD8+) T-Lymphozyten bestimmt. Die Angaben in Prozent beziehen sich jeweils auf die Gesamtheit der CD8positiven (CD8+) T-Zellen und stellen die Mittelwerte der einzelnen Gruppen dar. Für die nicht-immunisierte Kontrolle ergab sich der Wert 0,00% für doppelt-positive Zellen. (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; IFNγ+: Interferon-γ-positiv; CD: Differenzierungsmarker; n: Anzahl der Tiere; vp: virale Partikel) 80 4 Ergebnisse Spezifische Antikörper (mIU/ml) 70 63,5 60 50 40 30 20 10 0 0 1E+06 vp 1E+07 vp 1E+08 vp (n=2) (n=1) 0 (n=2) Abbildung 4.19 Antikörper-ELISA nach intramuskulärer Immunisierung mit AdHBsAg zur Ausweitung des Dosisbereichs An Tag 36 nach Vektorinjektion wurde jeweils zwei Mäusen der Gruppen 1-3 (s. Tabelle 4.6, S. 78) Blut entnommen und mittels ELISA der Antikörpertiter gegen HBsAg bestimmt. Dargestellt sind die Mittelwerte der einzelnen Gruppen. (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; ELISA: enzyme-linked immunosorbent assay; n: Anzahl der Tiere; vp: virale Partikel; mIU: 10-3 internationale Einheiten) 4.2.3 Immunisierung mit AdOVA Die Vektoren, die das Fusionsprotein T-OVA-EGFP exprimieren, wurden in vivo auf das Auslösen einer zellulären Immunantwort getestet. Hierbei wurden insbesondere die Immunantworten gegen unterschiedliche Antigene des Fusionsproteins untersucht. Immunantwort gegen Ovalbumin Für einen ersten Funktionstest von AdOVA wurden Mäuse des Stammes C57BL/6 gewählt. Diese haben den genetischen Hintergrund H2b und können das Kb-restringierte T-Zell-Epitop des Ovalbumins als fremd erkennen und eine entsprechende Immunantwort bilden. Die Gruppe bestand aus vier Mäusen und jeder Maus wurden pro Seite 1108 vp von AdOVA in einem Volumen von 50 µl in den Musculus tibialis anterior injiziert. Als Kontrolle diente eine nicht-immunisierte Maus. An Tag 13 wurden die 81 4 Ergebnisse Mäuse getötet und ihre Milzen entnommen. Zur Analyse der zellulären Immunantwort wurde eine Restimulation der T-Zellen mit einem Peptid des Ovalbumins (s. Abschnitt 3.7.4, S. 48) und eine anschließende Färbung gegen CD8 und intrazelluläres IFNγ durchgeführt. Nach Analyse im Durchflusszytometer war deutlich erkennbar, dass durch die Immunisierung mit AdOVA eine spezifische zelluläre Immunantwort in den Mäusen ausgelöst werden konnte (s. Abb. 4.20, S. 82). Für die nicht-immunisierte Kontrollmaus ergab sich ein Wert von 0,008% doppelt-positiver Zellen. 0,9 0,8 0,7 % CD8 IFN + + 0,6 0,5 0,4 0,3 0,2 0,1 0 K 1E+08 vp (n=1) (n=4) Abbildung 4.20 IFNγ-Assay (α-Ovalbumin) nach intramuskulärer Immunisierung von C57BL/6Mäusen mit AdOVA Vier Mäuse wurden mit 1108 viralen Partikeln (vp) immunisiert. An Tag 13 erfolgten die Milzentnahme und die Durchführung des IFNγAssays. Die Splenozyten wurden anschließend durchflusszytometrisch auf Ovalbumin-spezifische zytotoxische (IFNγ+CD8+) T-Zellen hin untersucht. Die Prozentzahlen beziehen sich jeweils auf die Gesamtheit der CD8-positiven (CD8+) T-Zellen und stellen die Mittelwerte der einzelnen Gruppen dar. Als Kontrolle (K) diente eine nicht-immunisierte Maus. (AdOVA: adenoviraler Vektor, der das Fusionsprotein T-OVAEGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; IFNγ+: Interferon-γ-positiv; CD: Differenzierungsmarker; α-Ovalbumin: Durchführung des IFNγ-Assays mit einem Ovalbumin-Pentamer; n: Anzahl der Tiere; C57BL/6: gezüchteter Mausstamm) 82 4 Ergebnisse Immunantwort gegen EGFP Die Immunantwort gegen einen anderen Teil des Fusionsproteins, das EGFP, wurde in Mäusen des Stammes BALB/c untersucht. Diese können durch ihren H2d-Hintergrund das Kd-restringierte T-Zell-Epitop des EGFP als fremd erkennen. Es wurden zwei Gruppen von Mäusen mit zwei unterschiedlichen Dosen des Vektors AdOVA immunisiert. Zum quantitativen Vergleich wurde eine weitere Gruppe von Mäusen mit dem Plasmid pSaV3 (s. Abb. 4.2, S. 55), das ebenfalls für das Fusionsprotein kodiert, immunisiert. Eine nicht-immunisierte Maus bildete die Negativkontrolle. Tab. 4.7, S. 83 zeigt den Injektionsplan. Alle Gruppen wurden an Tag 24 entsprechend dem Injektionsplan erneut immunisiert („Boost“). An Tag 35 wurde den Mäusen die Milz entnommen und analysiert. Tabelle 4.7 Vergleich der Immunantwort nach Injektion unterschiedlicher Vektordosen von AdOVA Lfd. Anzahl Nr. Mäuse Vektor/ Plasmid Vektordosis o. Plasmidmenge/Seite Injektionsroute 1 4 AdOVA 5108 vp i.m. 2 3 AdOVA 1,51010 vp i.m. 3 3 pSaV3 50 µg i.m. AdOVA: adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; pSaV3: für T-OVA-EGFP kodierendes Plasmid; i.m: intramuskulär; vp: virale Partikel; µg: Mikrogramm Die Analyse der spezifischen T-Lymphozyten mittels IFNγ-Assay zeigte in beiden Dosisbereichen eine deutlich ausgeprägte Immunantwort gegen das EGFP. Der Vergleich mit Injektion von Plasmid ergab eine starke Tendenz zu höheren spezifischen T-Zell-Zahlen bei Immunisierung mit viralen Vektoren; je nach Dosis um Faktor vier bis sechs. 83 4 Ergebnisse Die Anzahl doppelt positiver T-Zellen bei 1,51010 injizierten Vektorpartikeln betrug im Vergleich zur Dosis von 5108 Partikeln nur ca. zwei Drittel (s. Abb. 4.21, S. 84). Absolut gesehen war der Anteil der IFNγ-positiven T-Zellen in etwa gleich hoch wie bei der Immunisierung mit AdHBsAg. 0,35 0,3 % CD8 IFN + + 0,25 0,2 0,15 0,1 0,05 0 5E+08 vp 1,5E+10 vp Plasmid (n=4) (n=3) (n=3) Abbildung 4.21 IFNγ-Assay (α-EGFP) nach intramuskulärer Immunisierung und Boost mit AdOVA An Tag 35 nach Vektorinjektion wurde allen Mäusen der Gruppen 1-3 (s. Tabelle 4.7, S. 83) die Milz entnommen. Nach Durchführung des IFNγAssay wurden die Splenozyten durchflusszytometrisch auf EGFPspezifische zytotoxische (IFNγ+CD8+) T-Lymphozyten hin untersucht. Die Prozentangaben beziehen sich jeweils auf die Gesamtheit der CD8-positiven (CD8+) Zellen und stellen die Mittelwerte der einzelnen Gruppen dar. Als Kontrolle diente eine nicht-immunisierte Maus, für die sich der Wert 0,00% für doppelt-positive Zellen ergab. (AdOVA: adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; Plasmid: für T-OVA-EGFP kodierendes Plasmid; IFNγ+: Interferon-γ-positiv; CD: Differenzierungsmarker; α-EGFP: Durchführung des IFNγAssays mit einem EGFP-Pentamer; n: Anzahl der Tiere; vp: virale Partikel) 84 4 Ergebnisse 4.2.4 Zusammenfassung Die ersten Immunisierungsergebnisse zeigten, dass sich sowohl mit AdHBsAg als auch mit AdOVA Immunantworten auslösen ließen. Die Anzahl transgen-spezifischer zytotoxischer T-Zellen wurde sowohl im Pentamer- als auch im IFNγ-Assay gemessen und zeigte in allen Fällen eine Tendenz zu höheren Werten als bei Immunisierung mit Plasmid-DNA. Bei Immunisierung mit AdHBsAg wurde die humorale Antwort mittels ELISA gemessen. Ein Boost nach ca. sechs Wochen ergab Anhaltspunkte für eine Erhöhung der bereits bestehenden Immunantwort. 4.3 Vorläufige Ergebnisse aus weiterführenden Experimenten Aufgrund der vielversprechenden Ergebnisse aus der Charakterisierung in vitro und in vivo wurden erste Versuche mit Vektoren durchgeführt, deren Kapsid chemisch modifiziert worden war. Die Ergebnisse sollten jedoch noch durch größere Fallzahlen und Zusatzexperimente bestätigt werden und besitzen daher vorläufigen Charakter. Als erste Modifikation wurde eine PEGylierung durchgeführt. Diese Abschirmung der Vektoroberfläche soll verhindern, dass der Vektor seinen natürlichen Rezeptor CAR erkennt, der auf vielen verschiedenen Körperzellen (z.B. Hepatozyten) vorhanden ist. So könnte eine ungewollte Transduktion dieser Gewebe verhindert und das Sicherheitsprofil der Vektoren erhöht werden. Zusätzlich soll die PEG-Hülle einen Schutz vor bereits bestehenden, gegen das Kapsid gerichteten Antikörpern bilden. 4.3.1 PEGylierung von AdHBsAg Zunächst wurde der Vektor AdHBsAg PEGyliert (s. Abschnitt 3.5.15, S. 42). Es wurde ein 20 kDa NHS-PEG verwendet, das in HEPES-Puffer (50 mM, pH 8,0) gelöst wurde und anschließend in 80-fachem Überschuss über Aminogruppen auf der Virusoberfläche 85 4 Ergebnisse (18000/Vektorpartikel) zur Virussuspension gegeben wurde. Der elektrophil aktivierte N-Hydroxysuccinimidester reagiert hierbei unter Ausbildung einer stabilen Amidbindung und Freisetzung von N-Hydroxysuccinimid mit den Aminogruppen auf der Vektorpartikeloberfläche (s. Abb. 1.2, S. 15). Direkte Überprüfung der PEGylierung im Slot-Blot Im Slot-Blot (s. Abschnitt 3.5.11, S. 38) sollte der Effekt der PEGylierung auf die Transduktionsfähigkeit des Vektors AdHBsAg für A549-Zellen untersucht werden. Die Anzahl der detektierten Vektorgenome stellt hierbei ein Maß für die Infektiosität der Vektoren dar und sollte zwischen PEGylierten und nicht-PEGylierten Vektoren verglichen werden. Dazu wurden in einer 24-Loch-Platte 1105 A549-Zellen/Loch ausgesät und am nächsten Tag transduziert. Dies erfolgte in Doppelbestimmung mit jeweils 30 bzw. 120 MOI von AdHBsAg bzw. AdHBsAg-PEG. Nach einer Stunde wurde gründlich gewaschen und dann nach Protokoll (s. Abschnitt 3.5.11, S. 38) verfahren. Zur Kontrolle wurden die Gesamtpartikel aller zur Transduktion verwendeten Volumina bestimmt. Die Detektion der Genome erfolgte in beiden Fällen mit Hilfe einer Sonde gegen einen Teil des Fiber-Proteins. Abb. 4.22, S. 88 zeigt die Membran nach Auswertung im Phosphorimager. Hier ist deutlich erkennbar, dass die PEGylierten Vektoren wesentlich weniger infektiös sind als die Nicht-PEGylierten. Die Auswertung der Intensitätswerte (s. Tab. 4.8, S. 87) war aufgrund der teilweise sehr schwachen Signale schwierig. Sie ergab ein Absinken der Infektiosität durch PEGylierung auf deutlich < 5%. Die Kontrollen zeigen ähnlich hohe Gesamtpartikelzahlen für PEGylierte und nichtPEGylierte Vektoren, wobei die der PEGylierten sogar noch höher sind. 86 4 Ergebnisse Tabelle 4.8 Analyse des PEGylierungseffektes im Slot-Blot Intensitätsverhältnis AdHBsAg-PEG/AdHBsAg 30 MOI (0,12) * 120 MOI < 0,05 AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen exprimiert; PEG: Polyethylenglykol; MOI: Anzahl infektiöser Partikel pro Zelle; *durch Schwäche des Signals nicht ausreichend genau auswertbar 87 4 Ergebnisse 30 MOI 120 MOI - - AdHBsAg AdHBsAg -PEG + + Kontrolle (ohne Zellen) Abbildung 4.22 Slot-Blot zur Ermittlung des Einflusses der PEGylierung auf die Gentransfereffizienz in vitro A549-Zellen wurden in Doppelbestimmung mit jeweils 30 bzw. 120 infektiösen Partikeln pro Zelle von AdHBsAg (1. Zeile) und AdHBsAg-PEG (2. Zeile) transduziert. Als Kontrolle wurden die Gesamtpartikel der zur Transduktion verwendeten Volumina bestimmt (3. Zeile). Die Transduktionszeit betrug eine Stunde; zur Detektion der Vektorgenome wurde eine FiberSonde verwendet. (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen exprimiert; PEG: Polyethylenglykol; +: mit PEG; -: ohne PEG; A549: humane Lungenkarzinom-Zelllinie) 88 4 Ergebnisse Durchflusszytometrische Analyse der Transgenexpression Die Ergebnisse aus dem Slot-Blot (s. Abschnitt 4.3.1, S. 85) sollten durch Messung der Transgenexpression bei Transduktion von Zellen mit PEGylierten bzw. nicht-PEGylierten Vektoren bestätigt werden. Dazu sollten A549-Zellen entsprechend transduziert und anschließend durchflusszytometrisch analysiert werden. Da sich die Produktion von HBsAg schlecht messen lässt, wurde zunächst der Vektor AdOVA verwendet, da dieser bei Zelltransduktion durch das in der Expressionskassette enthaltene EGFP zu leicht detektierbarer Fluoreszenz der Zellen führt. In durchflusszytometrischen Vorexperimenten (Ergebnisse nicht gezeigt) wurde jedoch deutlich, dass die Fluoreszenz der mit AdOVA transduzierten A549-Zellen zu gering für eine verlässliche Nachweisbarkeit ausfiel. Dies fiel auch bei der Reinigung dieses Vektors im Dichtegradienten auf und ist darauf zurückzuführen, dass das EGFP hier in einem Fusionsprotein vorliegt [17]. Deshalb wurde zur Messung der Auswirkungen der PEGylierung auf die Transgenexpression der Vektor Ad1stGFP verwendet (s. Abschnitt 3.1.4, S. 20). Hierbei handelt es sich um einen Erstgenerationsvektor, der eine CMV-kontrollierte Expressionskassette für EGFP enthält. Dieser Vektor wurde parallel zu AdHBsAg unter Verwendung derselben Puffer- und PEGLösungen PEGyliert, was die Ergebnisse übertragbar macht. Um die Auswirkungen der PEGylierung auf die Transgenexpression in vitro zu überprüfen, wurden jeweils 2105 A549-Zellen in Doppelbestimmung mit unterschiedlichen Mengen des Vektors Ad1stGFP und Ad1stGFP-PEG transduziert. Nach 36 Stunden wurden die Zellen geerntet und im Durchflusszytometer die EGFP-Fluoreszenz gemessen. Als Maß für die Transgenexpression dient die mittlere Fluoreszenz aller Zellen. Bei den PEGylierten Vektoren ergab sich eine deutliche Abnahme der Zahl transduzierter Zellen im Vergleich zu nichtPEGylierten Vektoren. Berechnungen zufolge sinkt die Infektiosität durch PEGylierung auf ca. 0,1-0,2% im Vergleich zu nicht-PEGylierten Vektoren. Abb. 4.23 S. 90 zeigt die Ergebnisse der durchflusszytometrischen Messung. 89 4 Ergebnisse rel Transduktionseffizienz 1,2 1 0,8 ohne PEG 0,6 mit PEG 0,4 0,2 0 100 pMOI 300 pMOI Abbildung 4.23 Einfluss der PEGylierung auf die Transgenexpression in vitro A549-Zellen wurden in st Doppelbestimmung mit 100 und 300 pMOI von Ad1 GFP (schwarz) bzw. Ad1stGFP-PEG (gestreift) transduziert. 36 Stunden nach Transduktion erfolgte die Analyse im Durchflusszytometer. Als Kontrolle dienten nicht-transduzierte Zellen mit einem Wert von 0,03 bzw. 0,01. Zur Berechnung der relativen Transduktionseffizienz wurde jeweils der Wert der nicht-PEGylierten Vektoren gleich 1 gesetzt. (Ad1stGFP: adenoviraler Vektor, der grün fluoreszierendes Protein exprimiert; PEG: Polyethylenglykol; pMOI: Gesamtpartikel pro Zelle) 90 4 Ergebnisse 4.3.2 Immunisierung von Mäusen zum Vergleich zwischen PEGyliertem und nicht-PEGyliertem AdHBsAg Die folgenden Versuche sollten erste Aufschlüsse über die Auswirkungen einer PEGylierung in vivo geben. Hierzu wurden Mäuse (Stamm: BALB/c) mit jeweils gleichen Dosen der Vektoren AdHBsAg und AdHBsAg-PEG (s. Abschnitt 4.3.1, S. 85) immunisiert. Einer Vergleichs-gruppe wurde das Plasmid pCI/Ssmall, das ebenfalls für das HBsAg kodiert, injiziert. Nicht-immunisierte Mäuse dienten als Kontrolle. Tab. 4.9, S. 91 zeigt den Injektionsplan. Tabelle 4.9 Injektionsplan zum Vergleich von AdHBsAg und AdHBsAg-PEG in vivo Lfd. Anzahl Nr. Mäuse Vektor/ Plasmid VektordosisPlasmidmenge/ Seite Injektionsroute Applikationsvolumen [µl] 1 5 AdHBsAg 1108 vp i.m. 50 2 5 AdHBsAg-PEG 1108 vp i.m. 50 3 2 pCI/Ssmall 50 µg i.m. 50 AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; PEG: Polyethylenglykol; pCI/Ssmall: Plasmid, das für HBsAg kodiert; i.m: intramuskulär; vp: virale Partikel; µ: Mikro- An Tag 24 nach der ersten Injektion wurde dieselbe Vektordosis erneut verabreicht („Boost“). Nach weiteren 11 Tagen wurden die Mäuse getötet. Ihnen wurden die Milz für eine T-ZellAnalyse und die entsprechenden Muskeln für eine immunhistologische Untersuchung entnommen. Die zelluläre Immunantwort wurde über die Bestimmung der HBsAg-spezifischen zytotoxischen T-Lymphozyten mit dem Pentamer-Assay evaluiert (s. Abschnitt 3.7.4, S. 48). Bei den Mäusen, die mit PEGylierten Vektoren immunisiert worden waren, gab es deutliche Hinweise darauf, dass sie eine schwächere Antwort als die nicht-PEGylierten Vektoren 91 4 Ergebnisse ausbilden (ca. 50%). Betrachtet man jedoch die Infektiosität nach PEGylierung in vitro (s.o.) so fiel die Immunreaktion in Relation dazu überraschend stark aus. In Abbildung 4.24, S. 92 sind die Daten zusammengefasst. 4,5 4 % CD8+ Ld/S+ 3,5 3 2,5 2 1,5 1 0,5 0 AdHBsAg AdHBsAg+PEG Plasmid (n=5) (n=5) (n=2) Abbildung 4.24 Einfluss der PEGylierung auf T-ZellAntworten gegen das Transgen HBsAg in vivo An Tag 35 nach der Vektorinjektion (Boost an Tag 24) wurde allen Mäusen der Gruppen 1-3 (s. Tabelle 4.9, S. 91) die Milz entnommen. Anschließend wurden der Pentamer-Assay und eine durchflusszytometrische Analyse durchgeführt, bei der die Zahl HBsAg-positiver zytotoxischer (Ld/S+CD8+) T-Lymphozyten ermittelt wurde. Die Prozentzahlen beziehen sich jeweils auf die Gesamtheit der CD8-positiven (CD8+) Zellen und stellen die Mittelwerte der einzelnen Gruppen dar. Als Kontrolle dienten zwei nicht-immunisierte Mäuse, bei denen sich im Mittel der Wert 0,05% für doppelt-positive Zellen ergab. (AdHBsAg: adenoviraler Vektor, der das Hepatitis B Oberflächenantigen (HBsAg) exprimiert; PEG: Polyethylenglykol; Plasmid: für HBsAg kodierendes Plasmid; Ld/S+: positiv für das Pentamer Ld/S; CD: Differenzierungsmarker; n: Anzahl der Tiere) 92 4 Ergebnisse 4.3.3 Immunisierung von Mäusen zum Vergleich zwischen PEGyliertem und nicht-PEGyliertem AdOVA Auch der Vektor AdOVA wurde mit 80-fachem Überschuss eines 20 kDa-PEG über Aminogruppen auf der Virusoberfläche PEGyliert (s. Abschnitt 3.5.15, S. 42). Die Auswirkungen in vivo sollten durch Immunisierung von Mäusen (Stamm: BALB/c) evaluiert werden. Zwei Gruppen von Mäusen erhielten zwei verschiedene Vektordosen von PEGyliertem AdOVA. Als Vergleich diente neben den Mäusen, die den gleichen, nichtPEGylierten Vektor erhalten hatten (s. Abschnitt 4.2.3, S. 81), abermals die Immunisierung mit Plasmid-DNA (pSaV3); als Negativkontrolle wurden nicht-immunisierte Mäuse verwendet. Tab. 4.10, S. 93 zeigt den Injektionsplan. Tabelle 4.10 Injektionsplan zur Evaluation verschiedener Dosen von PEGyliertem AdOVA in vivo Lfd. Anzahl Nr. Mäuse Vektor/ Plasmid Vektordosis- o. Plasmidmenge/Seite Injektionsroute 1 4 AdOVA-PEG 5108 vp i.m. 2 4 AdOVA-PEG 1,51010 vp i.m. 3 3 pSaV3 50 µg i.m. AdOVA: adenoviraler Vektor, der das Fusionsprotein T-OVA-EGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; PEG: Polyethylenglykol; pSaV3: für T-OVA-EGFP kodierendes Plasmid; i.m: intramuskulär; vp: virale Partikel; µg: Mikrogramm An Tag 24 wurde den Mäusen dieselbe Vektordosis erneut injiziert („Boost“), 11 Tage später wurden ihnen die Milz zur Analyse spezifischer zytotoxischer T-Lymphozyten und die entsprechenden Muskeln für eine Immunhistologie entnommen. 93 4 Ergebnisse Die spezifischen zytotoxischen T-Lymphozyten wurden mit Hilfe des IFNγ-Assays bestimmt. Bei einer Dosis von 1108 vp war die Anzahl der positiven T-Zellen bei den PEGylierten Vektoren im Vergleich zu den nicht-PEGylierten Vektoren deutlich niedriger (ca. 50%), bei 1,51010 Partikeln deutete sich diese Tendenz nur an. Die Werte der PEGylierten Vektoren waren jedoch in beiden Fällen tendenziell höher als die der Plasmid-immunisierten Mäuse (s. Abb. 4.25, S. 94). 0,35 0,3 % CD8 IFN + + 0,25 0,2 ohne PEG mit PEG 0,15 0,1 0,05 0 5E+08 vp (n=4) 1,5E+10 vp (n=3/4) Plasmid 50 µg (n=3) Abbildung 4.25 Einfluss der PEGylierung auf T-Zell-Antworten gegen das Transgen T-OVA-EGFP in vivo An Tag 35 nach Immunisierung mit PEGyliertem AdOVA (Boost an Tag 24) wurde drei bzw. vier Mäusen jeder Gruppe (s. Tabelle 4.10, S. 93) die Milz entnommen, der IFNγ-Assay durchgeführt und die Splenozyten durchflusszytometrisch analysiert. Es wurde die Zahl der EGFPspezifischen zytotoxischen (IFNγ+CD8+) T-Zellen ermittelt. Die Angaben in Prozent beziehen sich jeweils auf die Gesamtheit der CD8-positiven (CD8+) T-Zellen und stellen Mittelwerte der einzelnen Gruppen dar. Dargestellt ist ein Vergleich zwischen nicht-PEGyliertem (schwarz) und PEGyliertem AdOVA (gestreift). Für die nicht-immunisierten Kontrollmäuse ergab sich im Mittel der Wert 0,00% für doppelt-positive Zellen. (AdOVA: adenoviraler Vektor, der das Fusionsprotein T-OVAEGFP (T: T-Antigen des Simian Virus 40, OVA: Ovalbumin, EGFP: modifiziertes grün fluoreszierendes Protein) exprimiert; PEG: Polyethylenglykol; Plasmid: für T-OVA-EGFP kodierendes Plasmid; vp: virale Partikel; n: Anzahl der Tiere; µg: Mikrogramm) 94 4 Ergebnisse 4.3.4 Immunhistologische Untersuchung von Muskelgewebe Um einen ersten Eindruck zu erhalten, welche Zellen bei intramuskulärer Injektion von AdHBsAg transduziert werden, wurden die an Tag 35 entnommenen Muskeln einiger Mäuse, die mit 1108 Vektorpartikeln immunisiert worden waren, immunhistologisch untersucht. Mit einem Antikörper gegen das HBsAg ließen sich jedoch keine positiven Zellen detektieren (Ergebnisse nicht gezeigt). Um zu erfahren, ob der Grund hierfür die fehlende Transduktion der Muskelzellen war, ob die Vektordosis zu klein war oder der Zeitpunkt der Entnahme zu spät erfolgte, wurden erneut Mäuse injiziert. In diesem Fall wurde der EGFP-exprimierende Vektor Ad1stGFP (s. Abschnitt 3.1.4, S. 20) verwendet, da sich bei ihm direkte Fluoreszenz der Zellen nachweisen lässt. Es wurden 11010 Partikel des Vektors injiziert, nach sechs Tagen erfolgte die Entnahme und die Fixierung des Muskels. Bei der Überprüfung im Fluoreszenzmikroskop ließen sich EGFP-positive Zellen detektieren (s. Abb. 4.26, S. 95). Abbildung 4.26 Gefrierschnitt des M. tibialis anterior einer Maus nach Injektion von 11010 Partikeln des Vektors Ad1stGFP Die Entnahme des Muskels erfolgte nach sechs Tagen. Links: Muskelgewebe im Durchlicht; rechts: gleicher Teil des Muskels unter Fluoreszenz (Ad1stGFP: adenoviraler Erstgenerationsvektor, der grün fluoreszierendes Protein exprimiert) 95 5 Diskussion 5 Diskussion 5.1 Konstruktion und Charakterisierung 5.1.1 Klonierung der Vektoren Die Konstruktion umfasste je nach Vektor zwei bis drei verschiedene Klonierungsschritte (s. Abschnitt 4.1, S. 52), wobei jeder Schritt durch eine Restriktionsanalyse der Plasmid-DNA mit verschiedenen Enzymen überprüft wurde. Die Restriktion der nach der Vektorreinigung isolierten Vektor-DNA mit HindIII ergab im Vergleich mit dem jeweiligen Ausgangsplasmid eine vollständige Übereinstimmung bis auf eine einzelne Bande, die eine Größe von ca. 2900 Basenpaaren aufwies. Diese entspricht dem Teil des Plasmids, der für die Propagierung in Bakterien notwendig ist und der durch die Linearisierung mit SwaI vor der Transfektion entfernt wird. Der Vektor Ad1Cysempty (aus pAd1CysPac) wurde mit dem Plasmid pGS66 verglichen, da sich die Nukleinsäuresequenzen von pGS66 und pAd1CysPac nur dadurch unterscheiden, dass pAd1CysPac für elf zusätzliche Aminosäuren im Fiber-Protein, zu denen auch das Cystein zählt, kodiert. Dadurch ergeben sich in der Restriktionsanalyse keine Unterschiede. Diese Ergebnisse zeigen, dass alle konstruierten Vektoren stabil sind. Es findet kein Rearrangement während der Amplifikation statt, so dass geschlossen werden kann, dass die viralen Sequenzen aus HBV auch im adenoviralen Kontext stabil bleiben. Das bedeutet weiterhin, dass die Vektoren amplifizierbar sind, was eine Grundvoraussetzung für ihre spätere Verwendung darstellt. 5.1.2 Titerbestimmung der Vektorpräparationen Zur Charakterisierung aller produzierten Vektoren wurden zunächst die infektiösen und die Gesamtpartikeltiter bestimmt (s. Tab. 4.1, S. 58). Alle Vektoren waren gleich gut amplifizierbar 96 5 Diskussion was sich in ähnlich hohen Titern (2-6108 Gesamtpartikel/µl) zeigte. Das bestätigte sich auch in der Berechnung der Vektorausbeute, der Anzahl an Vektorpartikeln je Produktionszelle. Hier ergaben sich Werte von 4000-10000 Vektorpartikeln/Produktionszelle, was im Bereich des Laborstandards liegt. Exemplarisch seien die Vektorausbeuten für Adempty (~7700 vp/Produktionszelle) und Ad1Cysempty (~7600 vp/Produktionszelle) genannt, die gleichzeitig zeigen, dass die cysteinhaltigen Vektoren keinen Nachteil in der Produktion haben. Die Amplifizierbarkeit der Vektoren ist eine wichtige Voraussetzung für ihre spätere Anwendung. Sie spricht u.a. dafür, dass keines der beiden Transgene so toxisch für die Produktionszellen ist oder mit der adenoviralen Replikation und Verpackung interferiert, dass sich dadurch Probleme bei der Vektorproduktion ergeben. 5.1.3 Nachweis der Transgenexpression AdHBsAg/Ad1CysHBsAg In Western-Transfer-Experimenten wurde ermittelt, ob die Vektoren ihr jeweiliges Transgen exprimieren. Zur Überprüfung der Vektoren AdHBsAg und Ad1CysHBsAg wurden A549-Zellen mit unterschiedlichen Mengen der beiden Vektoren transduziert, nach 48 Stunden geerntet und aufbereitet. Bei der Analyse der Proben konnte mit Hilfe eines Antikörpers gegen das HBsAg eine Doppelbande zwischen 25 und 30 kDa detektiert werden. Diese entspricht der nicht-glykosylierten (25 kDa) und der glykosylierten (30 kDa) Form des HBsAg und ist vielfach beschrieben worden [11, 26]. Die Glykosylierung ist in diesem Fall fakultativ und betrifft bis zu 40% der HbsAg-Partikel. Sie hat weder Einfluss auf deren Bildung noch auf ihre Sekretion und Immunogenität [24]. Die im Western-Transfer erhaltenen Ergebnisse zeigen, dass im verwendeten Dosisbereich bei höheren Vektormengen mehr Protein synthetisiert wird. Die Spezifität der Banden wurde durch die transduzierten und nicht-transduzierten Kontrollzellen bestätigt. Das Ziel dieses Versuchs war der Nachweis der Proteinsynthese in transduzierten A549Zellen. Da das HBsAg als sezerniertes Transgenprodukt mit dem intrazellulär stabilisierten Fusionsprotein T-OVA-EGFP verglichen werden soll, sollte außer der Synthese auch die 97 5 Diskussion Sezernierung des HBsAg durch transduzierte Zellen gewährleistet sein. Dazu müsste der Zellüberstand analysiert werden, wofür jedoch die Verwendung einer Leberzelllinie (im Gegensatz zu den hier verwendeten Lungenzellen) wesentlich sinnvoller erscheint. Da in diesem speziellen Fall für exakt dieselbe Expressionskassette des HBsAg das Stattfinden der Sezernierung mehrfach gezeigt wurde [33], wurden keine weiteren Analysen durchgeführt. AdOVA/Ad1CysOVA Auch die beiden Vektoren AdOVA und Ad1CysOVA, die das Fusionsprotein T-OVA-EGFP exprimieren, wurden im Western Transfer analysiert. Die Bande bei ca. 75 kDa, die bei Verwendung eines Antikörpers gegen den T-Antigen-Teil detektiert wurde, entsprach den Erwartungen und ließ sich nach „Strippen“ der Membran durch einen weiteren Antikörper gegen den EGFP-Teil des Fusionsproteins bestätigen. Unterschiedliche Proteinmengen bei 50 bzw. 100 MOI ließen sich auch in diesem Fall erkennen. Sowohl die transduzierte als auch die nicht-transduzierte Kontrolle zeigten, dass die Bande bei 75 kDa tatsächlich auf das Transgen in den beiden Vektoren zurückzuführen war. Da das Fusionsprotein unterschiedliche Antigene in sich vereint, ist der Vektor vielseitig einsetzbar. So können z.B. in verschiedenen Mausstämmen, die unterschiedliche Teile des Proteins als fremd erkennen, mit demselben Vektor Immunantworten ausgelöst werden. 5.1.4 Nachweis der intrazellulären Stabilisierung des Fusionsproteins Das Fusionsprotein T-OVA-EGFP, das von den Vektoren AdOVA und Ad1CysOVA exprimiert wird, wird über seinen T-Antigen-Teil intrazellulär durch Assoziation mit dem Hitzeschockprotein 73 stabilisiert [27]. Eine Co-Immunpräzipitation bestätigte diese Assoziation auch für Vektor-transduzierte Zellen. Durch Präzipitation mit einem Antikörper gegen den T-Antigen-Teil des Fusionsproteins wurde eine Proteinprobe gewonnen. In dieser ließen sich mit Hilfe zweier verschiedener Antikörper sowohl das Fusionsprotein (Antikörper gegen EGFP) als auch das Hitzeschockprotein 73 (Antikörper gegen hsp73) nachweisen. Die Assoziation dieser beiden 98 5 Diskussion Proteine in der Zelle muss also stattgefunden haben, da sonst das Hitzeschockprotein mit dem Antikörper gegen den T-Antigen-Teil nicht hätte co-immunpräzipitiert werden können. Diese intrazelluläre Stabilisierung könnte diverse Vorteile im Bezug auf die Stärke und die Qualität der Immunantwort haben. Reimann und Schirmbeck beschreiben in einem Übersichtsartikel [27] die Auswirkungen der Assoziation eines Proteins mit hsp73. Zum einen soll sich die Halbwertszeit des assoziierten Proteins verlängern. Zum anderen soll die Bindung von Epitopen an MHC I-Moleküle optimiert werden und gleichzeitig die Möglichkeit bestehen, dass das Protein in zusätzliche intrazelluläre Prozessierungswege eingeschleust werden kann. Die dadurch verlängerte und optimierte Präsentation des Antigens kann positive Auswirkungen auf die Stärke der Immunantwort haben, da mehr Zeit für die Aktivierung von Effektorzellen und Bildung von Antikörpern zur Verfügung steht. Zudem könnte sich durch die vielfältigere Prozessierung ein qualitativer Unterschied in der Immunantwort ergeben. Die konstruierten Vektoren ermöglichen eine Evaluation in vivo der Vorteile dieser Art von Transgenen und einen gleichzeitigen Vergleich mit der Immunantwort, die durch sezernierte Transgenprodukte ausgelöst wird. 5.1.5 Bestätigung der Existenz der eingeführten Cysteine Bei den modifizierbaren Vektoren Ad1CysHBsAg, Ad1CysOVA und Ad1Cysempty mussten aufgrund der genetisch eingeführten zusätzlichen Cysteinreste und den dadurch veränderten Produktionsbedingungen weitere Parameter überprüft werden. Die Existenz der Cysteinreste bestätigte sich hierbei zunächst in einem Größenunterschied der PCR-Produkte des Fiber-Fragments zwischen cysteinhaltigen und nicht-cysteinhaltigen Vektoren, der ca. 30-40 bp betrug. Er ließ sich auf die veränderte Nukleinsäuresequenz cysteinhaltiger Vektoren, die für elf zusätzliche Aminosäuren in der DNA kodiert, zurückführen (s. Abb. 4.10, S. 66). Außerdem ergab sich in den Sequenzvergleichen mit dem Kontrollvektor Ad1Cys eine komplette Übereinstimmung (s. Tab. 4.2, S. 67). 99 5 Diskussion Die zusätzlich eingeführten Cysteine bilden die Grundlage der Technologie zur genetischchemischen Modifikation von Vektoren. Sie erlauben die Kopplung verschiedener Arten von Liganden. So können beispielsweise Liganden mit einer Maleimid-Gruppe, die bei Reaktion mit dem Cystein eine Thioetherbindung ausbilden genausogut eingesetzt werden wie Liganden mit einer Dihydropyridylgruppe, die mit dem Cystein unter Bildung von Disulfidbrücken reagieren. Je nach Wahl des Liganden erlangt der Vektor die Möglichkeit, CAR-unabhängig zusätzliche Zelltypen transduzieren zu können. Die potenzielle Bioreversibilität der Kopplung unter Ausbildung von Disulfidbrückenbindungen könnte darüber hinaus eine effiziente Transduktion begünstigen, da nach der Endozytose eine Trennung von Vektor und Ligand erfolgen kann. Alle nachfolgend ablaufenden Prozesse, wie das Entkommen der Vektorpartikel aus dem Endosom und der effiziente Transport der DNA in den Nukleus, würden somit nicht durch den Liganden beeinträchtigt. Da die Anzahl der Cysteine bekannt ist, ist es zudem möglich, eine definierte Anzahl von Liganden zu koppeln. 5.1.6 Überprüfung cysteinhaltiger Vektorpräparationen auf Aggregatbildung In Gegenwart von Luftsauerstoff können sich zwischen den einzelnen Vektoren einer Suspension Disulfidbrücken und damit Vektor-Aggregate bilden. Da in diesem Fall keine chemische Kopplung an die Cysteinreste erfolgen kann (ohne den Einsatz von Reduktionsmitteln) stellt die Messung des Polydispersitätsindex einen wichtigen Schritt in der Qualitätskontrolle dar. Diese Methode gibt Aufschluss über die Größenverteilung der Partikel in einer Virussuspension, die im Fall einer Aggregatbildung nicht mehr homogen ist, was mittels photonenkorrelierter Spektroskopie gemessen werden kann. Der Polydispersitätsindex sollte in einer aggregatfreien Lösung kleiner 0,2 sein [15]. Tab. 4.3, S. 68 zeigt die gemessenen Werte, die alle unter 0,2 liegen und somit dafür sprechen, dass sich in der jeweiligen Lösung keine Aggregate gebildet haben. Gründe hierfür sind verwendete Reduktionsmittel in den ersten Abschnitten der Vektorreinigung und eine möglichst konstante gehaltene Argonatmosphäre. Diese wird vor 100 5 Diskussion allem im letzten Teil des Reinigungsprozesses notwendig, da hier mit Rücksicht auf eine evtl. spätere Kopplung von redoxsensitiven Liganden keine Reduktionsmittel mehr zugesetzt werden (s. Abschnitt 5.1.7, S. 101). 5.1.7 Bestimmung des Reduktionsmittelrestgehaltes in Virussuspensionen Reduktionsmittelreste, die am Ende des Reinigungsprozesses von Vektoren in der Virussuspension verbleiben, können im späteren Kopplungsprozess die Integrität redoxsensitiver Liganden beeinträchtigen und die Kopplungseffizienz beeinflussen. Beispiel für einen redoxsensitiven Liganden wäre Transferrin, dessen Struktur und damit Rezeptorbindungseigenschaften durch zahlreiche Disulfidbrücken stabilisiert werden. In Gegenwart größerer Mengen Reduktionsmittel würden die Disulfidbrücken reduziert und die Struktur des Liganden (und damit seine Funktion) verlorengehen. Genau wie die Messung des Polydispersitätsindex ist die Bestimmung des Reduktionsmittelrestgehaltes also ein wichtiger Schritt zur Überprüfung der Qualität einer Vektorpräparation. Zu diesem Zweck wird der Ellmann-Test eingesetzt, mit dem die Restmenge an Reduktionsmittel in der jeweiligen Suspension bestimmt werden kann. Die Werte für die cysteinhaltigen Vektoren sind in Tabelle 4.4, S. 70 angegeben und sind niedrig genug, um bei Kopplung redoxsensitiver Liganden deren Funktionalität nicht zu gefährden. Der Test wird normalerweise zum Nachweis von Thiolgruppen verwendet. So werden theoretisch in einer Suspension sowohl Reduktionmittel als auch freie Thiolgruppen der cysteinhaltigen Vektoren detektiert. Deren Konzentration ist allerdings im Verhältnis zu der des Reduktionsmittels so gering, dass sie vernachlässigt werden kann. Die Möglichkeit einer Verfälschung der Ergebnisse steigt somit mit der Konzentration des Vektors in der Suspension. 101 5 Diskussion 5.1.8 Zusammenfassung der Konstruktion und in vitro-Charakterisierung Die Ergebnisse aus Konstruktion und Charakterisierung zeigen ein Vektorsystem, das alle theoretischen Voraussetzungen erfüllt, um für genetische Vakzinierung eingesetzt werden zu können. Die Vektoren sind stabil und gewährleisten eine Produktion zu hohen Titern. Es werden zwei verschiedene Transgene exprimiert, von denen eines nachweislich intrazellulär mit hsp73 interagiert und hierdurch höchstwahrscheinlich stabilisiert wird. Durch den Vergleich von sezerniertem und intrazellulär verbleibendem Transgen kann evaluiert werden, ob und wie durch die Wahl der Art des Transgens Einfluss auf die Quantität und Qualität der Immunantwort genommen werden kann. Ebenso sind alle Voraussetzungen für verschiedene Kapsidmodifikationen wie Ligandenkopplung und PEGylierung und deren Kombination geschaffen, wodurch sich ein weiter Raum für ein großes Spektrum an Immunisierungsexperimenten zu unterschiedlichen Fragestellungen eröffnet. Aufgrund dieser vielversprechenden Ergebnisse wurden im Anschluss an die in vitroCharakterisierung erste Immunisierungsversuche mit AdHBsAg und AdOVA vorgenommen. Durch sie sollte gezeigt werden, dass in vivo Immunantworten ausgelöst werden können. Um im gleichen Zug einen Rahmen für weiterführende Experimente zu schaffen, wurden ein weiter Dosisbereich und mehrere Injektionsrouten getestet. 5.2 Immunisierungsversuche mit AdHBsAg und AdOVA 5.2.1 Immunisierung mit AdHBsAg zur Dosisfindung Um die Eignung des Gentransfersystems auch in vivo zu überprüfen, wurden erste Immunisierungsversuche mit AdHBsAg in Mäusen durchgeführt. Diese sollten zunächst dazu dienen, einen Überblick über sinnvolle Vektordosen zu bekommen. So wurden Mäuse über einen weiten Dosisbereich (zwischen 1106 und 11010 viralen Partikeln) immunisiert. In Anlehnung an übliche Impfrouten wurden die intramuskuläre und die subkutane Injektionsroute gewählt. Zum qualitativen und quantitativen Vergleich der Immunantwort mit 102 5 Diskussion einer durch ein nicht-virales Gentransfersystem ausgelösten, wurden Mäuse mit Plasmid-DNA (pCI/Ssmall), die dieselbe Expressionskassette enthält, immunisiert. Als Kontrolle dienten nicht-immunisierte Mäuse. Zelluläre Immunantwort gegen HBsAg Bei der Bestimmung im Pentamer-Assay zeigten alle immunisierten Mäuse T-Zell-Antworten gegen das HBsAg, die durch Vergleich mit den Negativkontrollen deutlich als spezifisch zu identifizieren waren. Es ergaben sich Anhaltspunkte für eine Korrelation zwischen der Stärke der Antworten und dem Anstieg der Dosen, wobei bei einer Dosis von 1107 Vektorpartikeln pro Muskel eine Schwelle anzusetzen war, unter der kaum noch positive T-Zellen gemessen werden konnten. Eine Prognose für höhere Dosen als die verwendeten 11010 Vektorpartikel ist schwierig, da mit der Anzahl der applizierten Vektorpartikel auch deren Toxizität steigt [1]. Hierzu sei verwiesen auf den Dosisvergleich bei der Immunisierung mit AdOVA (s. Abschnitt 4.2.3, S. 81), bei dem die Injektion von 1,51010 Vektorpartikeln eine niedrigere Anzahl doppelt-positiver T-Zellen ergab, als die von 5108 Partikeln, wobei der Grund dafür nicht abschließend geklärt ist. Die Immunisierung mit Plasmid-DNA schien der Vakzinierung mit adenoviralem Vektor quantitativ deutlich unterlegen. In den hier gezeigten Experimenten war die Zahl der durch die Plasmid-DNA induzierten HBsAg-spezifischen T-Lymphozyten im Vergleich zu der bei Injektion von Vektoren gemessenen um Faktor drei bis sieben schwächer, wobei die Menge an Plasmid-DNA, die zur Immunisierung verwendet wurde, dem Standard bei genetischer Vakzinierung mit Plasmiden entsprach [32]. Dieser Unterschied in der Gentransfereffizienz der beiden Systeme wird besonders deutlich, wenn man beachtet, dass der Vergleich in diesem Fall zwischen 1108 injizierten Vektorpartikeln und ca. 11013 injizierten Plasmidkopien stattfindet. Die Erklärung hierfür ist, dass die Aufnahme von DNA durch Zellen nur unspezifisch und zufällig erfolgt, während die Vektoren selbst aktive Mechanismen zur Zelltransduktion und zur Kernlokalisation ihrer DNA einsetzen. Zudem spielt vermutlich ein durch die Ad-Kapsidproteine vermittelter Adjuvanseffekt eine Rolle bei der Verstärkung der Immunantwort. 103 5 Diskussion Eine niedrigere Anzahl positiver T-Zellen bei Immunisierung mit Plasmid-DNA wurde ebenso wie die Abhängigkeit der Stärke der Immunantwort von der Vektordosis auch schon bei Primaten beschrieben [3]. Der Nachweis der IFNγ-Produktion bei Restimulation der Zellen mit einem Peptid des HBsAg ergab qualitativ die gleiche Tendenz wie der Pentamer-Assay. Diese Methode entsprach zusätzlich einem ersten Funktionstest der CTL. Daten in vergleichbarer Größenordnung wurden auch durch Reyes-Sandoval et al [28] bei Immunisierung von Mäusen mit Ad5 gegen das HIV-gag-Protein erhoben und in einem Übersichtsartikel von Tatsis und Ertl [39] beschrieben. Eine direkte Untersuchung der CTL auf lysierende Wirkung im sog. „Killing Assay“ steht noch aus. Außerdem wäre zu klären, welcher Vorgang letztendlich ausschlaggebend für die Auslösung dieser Immunantwort ist. Bei intramuskulärer Injektion des Vektors bestünde eine Möglichkeit in der CAR-vermittelten Transduktion von Muskelzellen. Hierbei stellt sich dann die Frage, ob es eine positive Korrelation zwischen der Anzahl transduzierter Muskelzellen und der Höhe der Immunantwort gibt. Da reife Muskelzellen jedoch generell schlecht mit Ad5 transduzierbar sind und durch eine geringe Anzahl an MHC I-Komplexen auch schlecht präsentieren, könnte die Transduktion von anderen Zellen über CAR bzw. αv-Integrine (z.B. Fibroblasten, dendritische Zellen) ebenfalls eine Rolle spielen. Genauso wäre die CARunabhängige Aufnahme der Vektorpartikel durch Zellen des Immunsystems über andere Rezeptoren (z.B. Scavenger-Rezeptor) und deren Transduktion denkbar. Um sowohl der Frage nach dem Stattfinden der CAR-vermittelten Muskeltransduktion als auch dem Mechanismus der Dosisabhängigkeit nachzugehen, wurden bereits erste histologische Untersuchungen mit entnommenen Muskeln durchgeführt. Histologische Untersuchungen Nach einer Entnahme der Muskeln an Tag 35 nach 8 Injektion von 110 Vektorpartikeln von AdHBsAg konnten immunhistologisch mit einem Antikörper gegen das HBsAg keine positiven Zellen detektiert werden. Um zu erfahren, ob der Grund hierfür die fehlende Transduktion der Muskelzellen war, ob die Vektordosis zu 104 5 Diskussion klein war oder der Zeitpunkt der Entnahme zu spät erfolgte, wurde Mäusen der Vektor Ad1stGFP injiziert (11010 Partikel, i.m.). Nach sechs Tagen erfolgte die Entnahme und die Fixierung des Muskels. Bei der Überprüfung im Fluoreszenz-Mikroskop ließen sich EGFPpositive Zellen detektieren (s. Abb. 4.26, S. 95). Nachdem auch in der Literatur ein Abfall der Transgenexpression innerhalb kurzer Zeit erwähnt wird (Abfall der β-GalaktosidaseExpression (5108 Vektorpartikel i.m.) unter die Detektionsgrenze innerhalb von 30 Tagen [43]), scheinen die späte Entnahme und evtl. auch die niedrige Dosis ein Grund für die negativen Ergebnisse aus den ersten immunhistologischen Untersuchungen der mit AdHBsAg transduzierten Muskeln zu sein. Für weitere Untersuchungen zum Verhältnis zwischen Stärke der Immunantwort und Anzahl der transduzierten Muskelzellen müssen also höhere Vektordosen injiziert werden und die Muskelentnahme muss zu einem früheren Zeitpunkt erfolgen. Humorale Immunantwort gegen HBsAg Auch im Fall der humoralen Immunantwort gegen HBsAg gab es Hinweise auf eine Dosisabhängigkeit. Bei 1108 injizierten Vektorpartikeln konnte ein niedriger Antikörpertiter gemessen werden, der sich bis hin zu 11010 Partikeln steigerte, jedoch in keinem der Fälle höher war als der der DNAimmunisierten Mäuse. Eine Schwelle, wie sie bei der zellulären Immunantwort gezeigt wurde, konnte nicht eindeutig definiert werden. Gründe für die eher schwache Ausprägung der humoralen Antwort könnten eine ineffiziente Produktion bzw. Ausschleusung des Antigens durch die transduzierten Zellen sein. Aufgrund dessen wäre es denkbar, dass der Kontakt zu B-Zellen und damit deren Aktivierung nicht in ausreichendem Maß zustande kam und/oder dass nicht genügend antigenpräsentierende Zellen wie z.B. Makrophagen das Protein aufnehmen und auf ihren MHC II-Komplexen präsentieren konnten. Dieser Vorgang führt zur Aktivierung CD4-positiver T-Helferzellen, die ebenfalls zur Antikörperproduktion benötigt werden. In der Literatur ist hingegen von einer Überlegenheit viraler Vektoren über Plasmid-DNA bei der Auslösung von Antikörperantworten die Rede. Mascola et al [19] beschreiben im Vergleich von Plasmid-DNA und adenoviralem Vektor nach intramuskulärer Immunisierung 105 5 Diskussion von Rhesusaffen gegen das HIV-gag-Protein eine wesentlich stärkere humorale Antwort auf den Vektor als auf DNA. Bei Worgall et al wird nach Immunisierung von C57BL/6-Mäusen mit 1108 bzw. 1109 Partikeln eines β-Galaktosidase exprimierenden Vektors eine starke humorale Antwort erzielt [42]. Auch in einem Übersichtsartikel [39] wird eine höhere Antikörper-Antwort durch virale Vektoren als durch Plasmid-DNA erwähnt. Ein möglicher Grund für diesen Unterschied zwischen den gezeigten Experimenten und der Literatur ist die Verwendung unterschiedlicher Immunisierungsschemata. Neben dem Versuch, die Ursache dafür zu finden, dass in den durchgeführten Experimenten der Vektor eher schwächere humorale Immunantworten auszulösen schien als das Plasmid, sollten die Antikörper zusätzlich in einem Neutralisationstest auf Funktion überprüft werden. 5.2.2 Vergleich von intramuskulärer und subkutaner Injektionsroute In Anlehnung an gängige Immunisierungsrouten wurden in diesem Versuch Immunantworten nach intramuskulärer bzw. subkutaner Injektion verglichen. Diese waren in beiden Fällen ähnlich, tendenziell waren sie nach subkutaner Immunisierung, insbesondere nach dem Boost, etwas stärker ausgeprägt. Das könnte sich auf die große Anzahl antigenpräsentierender Zellen (Langerhanszellen) zurückführen lassen, die sich in der Epidermis befinden und sowohl den zellulären als auch den humoralen Zweig des Immunsystems aktivieren können. Alles in allem waren die Unterschiede marginal, so dass sich aus diesen Ergebnissen keine zwingende Entscheidung für eine der beiden Routen ergab. Das wird auch von Casimiro et al [4] bestätigt, nachdem bei Experimenten mit Affen, die mit 11011 adenoviralen Partikeln gegen das HIV-gag-Protein immunisiert worden waren, im Vergleich von subkutaner und intramuskulärer Injektionsroute kein Unterschied in der Stärke der Immunantwort festgestellt werden konnte. 106 5 Diskussion 5.2.3 Boost-Experiment Der Boost, d.h. die erneute Injektion desselben Impfstoffes einige Zeit nach der ersten Immunisierung, ist Bestandteil vieler Immunisierungsprotokolle. Der Effekt besteht in einer Steigerung der bereits bestehenden Immunantwort und damit in einem besseren Impfschutz. In den vorliegenden Experimenten erfolgte die zweite Injektion von AdHBsAg jeweils in einem Zeitraum von vier bis sechs Wochen nach der ersten. Die starke Tendenz zu höheren T-Zell-Antworten und Antikörpertitern bei der Messung nach dem Boost zeigte dessen positive Wirkung. Bekräftigt wurde dies durch T-Zell-Analysen bei Mäusen, die nur eine Injektion erhalten hatten und zum Zeitpunkt der zweiten Messung einen deutlichen Abfall der CTL-Werte aufwiesen (Ergebnisse nicht gezeigt). Die Mäuse, die mit den niedrigsten Vektordosen immunisiert worden waren, zeigten nach dem Boost weder eine Erhöhung der Antikörpertiter gegen HBsAg noch der spezifischen T-Zell-Antwort. Das war zu erwarten, da der Erfolg des Boostes darauf basiert, dass bereits Effektorzellen des Immunsystems vorhanden sind, die das Antigen kennen und entsprechend stark reagieren. Da sich nach der ersten Vektorgabe neutralisierende Antikörper gegen das adenovirale Kapsid bilden [3, 6, 44], was im vorliegenden Fall durch Neutralisationstests noch bestätigt werden sollte, stellt sich nun die Frage nach dem Grund für die Erhöhung der Immunantwort nach dem Boost. Eine Erklärung besteht in der Vermutung, dass die erfolgreiche zweite Vektorgabe mit anschließender Erhöhung der Antigen-spezifischen T-Zellen und Antikörper von der verwendeten Injektionsroute abhängt. Bei intravenöser Applikation wurden vielfach Misserfolge im Hinblick auf schwache Transduktionseffizienzen bei wiederholten Vektorgaben beschrieben [8]. Im Gegensatz dazu führte die intramuskuläre Injektion bei bestehender Immunität gegen das Adenovirus durchaus zur Transduktion von Muskelzellen (evtl. wegen schlechterer Zugänglichkeit der Antikörper zu den Vektorpartikeln) [6]. Geht man davon aus, dass die Stärke der Immunantwort mit der Zahl CAR-vermittelt transduzierter Zellen zusammenhängt, so könnte der Erfolg des Boostes durch die Verwendung der intramuskulären Injektionsroute erklärt werden. 107 5 Diskussion Eine weitere Überlegung wäre, dass zur nochmaligen Anregung des Immunsystems durch Boost nur eine geringe Menge an Vektorpartikeln (bzw. in der Folge davon nur eine geringe Zahl transduzierter Zellen) benötigt wird. So könnten die wenigen Partikel, die nach der Neutralisation übrig bleiben, für eine Erhöhung der Immunantwort ausreichen. Zu dieser Hypothese gelangen auch Casimiro et al [4], die in diesem Zusammenhang ein Experiment beschreiben, bei dem Affen mit adenoviralen Vektoren gegen das HIV-gag-Protein immunisiert worden waren und dadurch neutralisierende Antikörper gegen das Adenovirus gebildet hatten. Nach erneuter Injektion konnte trotzdem ein Anstieg der Transgenspezifischen zellulären Immunantwort beobachtet werden. Eine ganz andere Hypothese dafür, dass trotz neutralisierender Antikörper gegen das Vektorkapsid eine Steigerung der Immunantwort und damit ein wirksamer Boost zustande kommt, wäre die folgende: Antikörper des Typs IgG haben opsonisierende Funktion. Das heißt, dass die Phagozytose von Fremdkörpern, an die Immunglobuline der Klasse G gebunden sind, in hohem Maße verstärkt wird. Dies kommt u.a. über die Bindung des Fc-Teils der Antikörper an die Fcγ-Rezeptoren auf Makrophagen zustande. So könnten auch VektorIgG-Komplexe verstärkt durch Makrophagen phagozytiert werden. Im Phagosom entsteht durch die Verschmelzung mit einem Lysosom zum Phagolysosom ein saures Milieu, das eine wichtige Voraussetzung für die Zerlegung des adenoviralen Kapsids und das Freiwerden der DNA darstellt (s. Abschnitt 1.3.3, S. 8). So könnte es zur Transduktion von Makrophagen und zur Transgenproduktion kommen, was im Endeffekt wieder zu einer Präsentation von Peptiden auf MHC-Komplexen und der damit verbundenen Aktivierung des adaptiven Immunsystems führt, unabhängig von einem CAR-vermittelten Mechanismus. Zur Überprüfung dieser Überlegung müssten zunächst adenovirale Vektoren mit neutralisierenden Antikörpern inkubiert werden. Diese vorinkubierten Partikel sollten zu isolierten Makrophagen gegeben werden, die dann einige Stunden später auf Transgenexpression (z.B. in Form von Fluoreszenz) untersucht werden. Damit könnte gezeigt werden, dass opsonierte Partikel zur Transduktion von Makrophagen (und evtl. auch anderen antigenpräsentierenden Zellen) befähigt sind. Zudem wären weitere Analysen über die Dauer 108 5 Diskussion der Transgenexpression in den Makrophagen und die Möglichkeit der Auslösung einer sekundären Immunantwort durch diesen Mechanismus notwendig. Keine dieser Überlegungen schließt ein paralleles Auftreten der verschiedenen Mechanismen aus. Ihre Bedeutung wird jedoch in den jeweiligen Ansätzen unterschiedlich gewichtet. 5.2.4 Immunisierung mit AdOVA Zum Abschluss der ersten in vivo-Überprüfung wurde ein Vektor, der das Fusionsprotein T-OVA-EGFP exprimiert (AdOVA), auf seine Eignung zur Auslösung von Immunantworten getestet. Es wurde ein Dosisvergleich durchgeführt, der jedoch kein kontinuierliches Spektrum, sondern nur eine relativ niedrige Dosis (5108 Vektorpartikel) und eine sehr hohe Dosis (1,51010 Vektorpartikel) umfasste. Das Fusionsprotein T-OVA-EGFP kann bei Injektion des Vektors AdOVA je nach Mausstamm entweder eine Immunantwort gegen den Ovalbumin-Teil oder gegen das EGFP auslösen. Zunächst erfolgte die Immunisierung von Mäusen des Stammes C57BL/6, in denen sich zytotoxische T-Lymphozyten gegen das Ovalbumin bildeten. Durch Vergleich mit der Negativkontrolle konnten diese als spezifisch eingestuft werden. Die Immunisierung von BALB/c-Mäusen mit AdOVA ergab spezifische T-Lymphozyten gegen den EGFP-Teil. Deren Anzahl war um das Vier- bis Sechsfache höher als die in den Mäusen, die eine Injektion mit Plasmid-DNA erhalten hatten. Die hier verwendeten unterschiedlichen Vektordosen führten zu einem überraschenden Ergebnis. Die T-Zell-Antwort bei Injektion von 5108 Vektorpartikeln schien wesentlich höher als die bei Injektion von 1,51010 Partikeln gemessene. Das steht im Gegensatz zu der in den ersten Experimenten mit AdHBsAg vermuteten Dosisabhängigkeit. Die Verwendung eines anderen Vektors und eine AdHBsAg-Höchstdosis von 11010 Vektorpartikeln erschweren jedoch die Übertragbarkeit der Ergebnisse. Eine Erklärung wäre die Zunahme der 109 5 Diskussion direkten Toxizität bei Applikation von erhöhten Dosen und eine daraus hervorgehende Beeinflussung der Immunantwort. So könnte das überexprimierte intrazellulär verbleibende transgene Protein, das zudem durch hsp73 stabilisiert ist, schon aufgrund der erhöhten Konzentration in der Zelle eine toxische Wirkung entfalten, die beim sezernierten transgenen Protein nicht beobachtet wird. Möglich wäre auch, dass sich durch die hohe Vektordosis bei 1,51010 Vektorpartikeln eine entsprechend hohe antiadenovirale Antwort bildet [20], die zu einer Neutralisation der Vektorpartikel beim Boost führt. Aufgrund dessen wäre hier die Anzahl positiver T-Zellen niedriger als bei Mäusen mit 1108 Partikeln, da der Boost bei diesen wirksam war. Diese Überlegung wäre durch die Auswertung der Antikörpertiter in Seren vor und nach dem Boost zu bestätigen bzw. abzulehnen. Träfe die Hypothese zu, so müssten die Antikörpertiter vor dem Boost bei den Mäusen mit einer Dosis von 1,51010 Vektorpartikeln höher sein als bei denen mit 5108 Partikeln. Ein anderes Ergebnis spräche möglicherweise für die erhöhte Toxizität bei höherer Dosis. Diese Ergebnisse runden die Charakterisierung der Vektoren ab. Zusätzlich zur Tauglichkeit in vitro konnte gezeigt werden, dass nach Injektion der Vektoren auch in vivo Immunantworten gegen das jeweilige Transgen gebildet werden können. Die Ergebnisse zeigen die Aktivierung des humoralen und des zellulären Zweiges und lassen sich in zahlreichen Vergleichen mit der Literatur in einen großen Zusammenhang einordnen. Es gab deutliche Anhaltspunkte dafür, dass sich die vielfach beschriebene Überlegenheit adenoviraler Vektoren über DNA-Vakzinen bestätigen lässt. Ebenso wiesen die Ergebnisse auf eine Dosisabhängigkeit der Anzahl spezifischer T-Lymphozyten und Antikörper hin. Dies wurde jedoch durch das Ergebnis der Immunisierung mit AdOVA (eine höhere Vektordosis ergab hier eine niedrigere Anzahl positiver T-Zellen) eingeschränkt. Durch die zahlenmäßig kleinen Gruppen konnten jedoch bislang nur Tendenzen gezeigt werden. Um verlässlichere Daten zu erheben und diese Ergebnisse zu verifizieren, sollten die Experimente in jedem Fall in größerem Maßstab (Gruppengröße > 10) wiederholt werden. 110 5 Diskussion Dadurch, dass bei diesen Vektoren zusätzlich die neue Technologie für chemische Kapsidmodifikationen angewendet werden kann, eröffnen sich vielfältige Möglichkeiten für Experimente, die ihr Ziel in der Verbesserung von Effizienz und Sicherheit genetischer Vakzinierung haben. Das Wissen um einen sinnvollen Dosisbereich und Injektionsrouten erleichtert den Einstieg in solche neuen Experimente, von denen einige, die allerdings noch vorläufigen Charakter besitzen, im nächsten Abschnitt besprochen werden. 5.3 Modifikation von AdHBsAg und Ad1CysHBsAg 5.3.1 PEGylierung von AdHBsAg In vorläufigen Experimenten wurde zunächst der Vektor AdHBsAg PEGyliert. Die Auswirkungen dieser PEGylierung wurden in einem Slot-Blot analysiert, der Auskunft über die Anzahl der Virusgenome gibt, die von Zellen aufgenommen werden. Es wurde der nichtmodifizierte Vektor AdHBsAg mit dem modifizierten Vektor AdHBsAg-PEG verglichen. Hierbei konnten in Zellen, die mit nicht-PEGyliertem AdHBsAg transduziert worden waren, deutlich mehr Vektorgenome detektiert werden als in den Zellen, die PEGylierten AdHBsAg erhalten hatten. Die Quantifizierung der Ergebnisse erbrachte eine Senkung der aufgenommenen Vektorgenome auf deutlich < 5% im Vergleich zu nicht-PEGylierten Vektoren. Eine Kontrollreihe zeigte, dass der Grund hierfür nicht in der Verwendung unterschiedlicher Vektordosen zu suchen war. Dort wurde die Gesamtpartikelzahl der zur Transduktion verwendeten Vektormengen bestimmt. Diese war beim PEGylierten Vektor sogar höher als beim Nicht-PEGylierten. Anzumerken ist, dass dieses Experiment nicht zur Überprüfung der inversen Bioaktivität geeignet ist, da ein Vergleich zwischen Vektormengen im Slot-Blot-Verfahren nur zulässig ist, wenn jede Probe mit bzw. ohne Zelltrümmer aufgetragen wird. So ist die Signalstärke nach dem Auftragen von Partikeln ohne Zelltrümmer wesentlich stärker als mit Zelltrümmern, da 111 5 Diskussion diese einen nicht zu vernachlässigenden Teil der Bindungsstellen auf der Membran besetzen, so dass in Anwesenheit der Zellen von vornherein weniger DNA gebunden werden kann [14]. Da im Slot-Blot nur gezeigt werden konnte, wie sich die PEGylierung auf die Aufnahme der Vektorgenome in die Zelle auswirkt, aber keine Aussage über die Transduktionseffizienz möglich war, wurde ein weiterer Versuch durchgeführt. In diesem wurden Zellen mit einem EGFP-exprimierenden Erstgenerationsvektor (Ad1stGFP), der nach exakt gleichem Protokoll wie AdHBsAg modifiziert worden war, transduziert. Die durchflusszytometrische Analyse dieser Zellen ergab ein deutliches Absinken der Transduktionseffizienez durch PEGylierung. Das wurde darauf zurückgeführt, dass der Vektor durch die PEG-Hülle nicht mehr an seinen natürlichen Rezeptor CAR binden bzw. nicht mehr in die Zelle aufgenommen werden kann [15]. Durch die absolute Gleichbehandlung der Vektoren Ad1stGFP und AdHBsAg sollte dieses Ergebnis auf AdHBsAg übertragbar sein und bestätigt so das im Slot-Blot erhaltene Ergebnis. Bei O’Riordan et al wird eine Reduktion der Infektiosität von PEGylierten Vektoren erwähnt [23]. Genauso beschreiben Kreppel et al eine starke Erniedrigung der Transduktionseffizienz PEGylierter Vektoren in vitro [15]. Croyle et al erwähnen, dass PEGylierte Vektoren sich in ihrer Transduktionseffizienz in vitro nicht von Nicht-PEGylierten unterscheiden [8], was jedoch in diesem Fall sicher daran liegt, dass die PEGylierung mit einem wesentlich geringeren Überschuss von PEG über Oberflächenaminogruppen durchgeführt wurde. Außerdem wurden in dieser Studie andere aminoreaktive Gruppen als Succinimidylpropionsäureester verwendet. 5.4 Immunantwort bei PEGylierten und nicht-PEGylierten Vektoren Die Idee der PEGylierung umfasst mehrere Aspekte. Durch das Polymer-Schild sollen die Vektorpartikel vor der Neutralisation durch bereits vorhandene antiadenovirale Antikörper 112 5 Diskussion geschützt werden. Diese können sowohl aus einer vorangegangenen natürlichen Infektion stammen als auch nach einer bereits erfolgten Vektorgabe gebildet worden sein. Besteht noch keine Immunität gegen das Adenovirus, soll die PEGylierung zudem die Antikörperbildung gegen das Kapsid vermindern. Dadurch soll eine effiziente und unproblematisch wiederholbare Vektorgabe ermöglicht werden. Der starke Infektiositätsverlust bei PEGylierten Vektoren in vitro wurde darauf zurückgeführt, dass das PEG die Bindung des Vektors an seinen natürlichen Rezeptor CAR erheblich beeinträchtigt. In der Annahme, dass die Immunantwort mit der Zahl von Zellen zusammenhängt, die CAR-vermittelt transduziert werden, wurde daraufhin auch eine starke Reduktion der Immunantwort in vivo erwartet. Der Vergleich zweier Gruppen von Mäusen, von denen die eine mit PEGylierten, die andere mit nicht-PEGylierten Vektoren immunisiert worden war, ergab in beiden Fällen eine zelluläre Immunantwort. Quantitativ war diejenige der PEGylierten Vektoren ca. halb so stark wie bei nicht-PEGylierten Vektoren. Die Differenz beider Gruppen war also wesentlich geringer als die in vitro erhobenen Daten es vermuten ließen. Geht man davon aus, dass für die Auslösung einer Immunantwort die Transgenexpression eine Rolle spielt, so kann man aufgrund der in vitro Daten annehmen, dass diese durch PEGylierung auf ca. 5% des Ausgangswertes sinkt. Eine Injektion von 1108 PEGylierten Vektorpartikeln entspräche somit der Injektion von 5106 nicht-PEGylierten Partikeln. Im Hinblick auf die Schwelle zur Induktion einer Immunantwort, die in einem ersten Experiment mit verschiedenen Dosen von AdHBsAg bei 1107 Partikeln determiniert worden war, ist das Ergebnis der PEGylierten Vektoren umso überraschender. Das Resultat bestätigte sich im Vergleich von PEGylierten und nicht-PEGylierten AdOVAVektoren, der in zwei verschiedenen Dosisbereichen durchgeführt wurde. Die Immunantwort bei PEGylierten Vektoren entsprach ebenfalls ca. 50% von der der nicht-PEGylierten. Dadurch, dass die jeweiligen Immunisierungen mit verschiedenen Vektoren erfolgten, die unterschiedliche Transgene exprimieren und in verschiedenen Dosisbereichen verwendet wurden, gewinnt das Ergebnis an Bedeutung. 113 5 Diskussion Zudem ergaben sich erste Hinweise im Hinblick auf die in Abschnitt 5.2.1, S. 102 gestellte Frage nach dem für die Auslösung der Immunantwort verantwortlichen Prozess. Die schwache Infektiosität in vitro und die im Verhältnis starke Ausprägung der Immunantwort bei PEGylierten Vektoren lässt vermuten, dass die Höhe der Immunantwort nicht allein von der Zellzahl abhängt, die CAR-vermittelt transduziert wird. Wäre dies der Fall, so würde man eine wesentlich stärkere Reduktion der Immunantwort erwarten. Es erscheint eher plausibel, dass zumindest ein Teil der Vektoren durch Makrophagen, dendritische Zellen etc. CARunabhängig aufgenommen wird und es durch deren Transduktion zu einer Immunantwort kommt, da dieser Prozess wahrscheinlich durch die PEGylierung wenig beeinträchtigt wird. Denkbar wäre z.B. eine Aufnahme PEGylierter Partikel über Scavenger-Rezeptoren Unter der Annahme eines Zusammenspiels von CAR-vermittelter Transduktion und CARunabhängiger Aufnahme der Vektoren durch Zellen des Immunsystems ließe sich das beobachtete Phänomen am besten erklären: So wäre es durchaus möglich, dass einerseits durch die Transduktion von Makrophagen und dendritischen Zellen eine Immunantwort durch PEGylierte Vektoren ausgelöst wird und andererseits durch die verminderte CARvermittelte Transduktion von (Muskel-) Zellen aufgrund der PEGylierung ein quantitativer Unterschied zu nicht-PEGylierten Vektoren besteht. Wie bereits im Abschnitt 5.2.1, S. 102 erwähnt, wäre also eine (immun-) histologische Untersuchung der injizierten Muskeln sinnvoll. Durch den Vergleich zwischen PEGylierten und nicht-PEGylierten Vektoren ließe sich auf diese Weise einfach herausfinden, ob sich die Anzahl der transduzierten Muskelzellen verändert. Eine Analyse der regionalen Lymphknoten sollte folgen, da die aktivierten Zellen des Immunsystems dorthin migrieren. Im nächsten Schritt sollte überprüft werden, ob das Polymer-Schild vor Antikörperbildung gegen das adenovirale Kapsid schützt. Hierzu eignet sich eine Untersuchung des Serums auf neutralisierende Antikörper gegen das Adenovirus, die im positiven Fall entweder gar nicht vorhanden bzw. zumindest niedriger sind als bei Immunisierung mit nicht-PEGylierten Vektoren. Die Möglichkeit der Vektorgabe bei bestehender Immunität gegen das Adenovirus könnte folgendermaßen evaluiert werden: Zunächst sollte eine Vorimmunisierung gegen das 114 5 Diskussion Adenovirus mit dem leeren, kein Transgen exprimierenden adenoviralen Vektor Adempty stattfinden, anschließend die Injektion von AdHBsAg bzw. AdHBsAg-PEG erfolgen. Durch einen quantitativen Vergleich der ausgelösten HBsAg-spezifischen Immunantworten sollte es möglich sein, den Effekt der PEGylierung im Hinblick auf die Neutralisation durch bereits vorhandene antiadenovirale Antikörper zu bestimmen. Aus diesem Ergebnis könnten sich nachfolgend auch Hinweise auf die Effekte der antiadenoviralen Antikörper auf die Immunisierung ergeben. Die intravenöse Gabe eines PEGylierten Vektors nach Vorimmunisierung wurde bereits von Croyle et al erfolgreich durchgeführt [8]. Der PEGylierte Vektor ermöglichte eine effiziente wiederholte Gabe des Vektors, trotz in diesem Fall wesentlich geringerem PEGylierungsgrad. 5.5 Perspektive Die gezeigten Ergebnisse geben nur einen kleinen Einblick in die experimentellen Möglichkeiten, die die konstruierten Vektoren bieten. Alle Vektoren ermöglichen die Induktion von spezifischer humoraler und zellulärer Immunantwort, die ihren Schwerpunkt auf der zellulären Seite hat, was den Zielen der genetischen Vakzinierung entspricht. Zahlreiche Hinweise auf die quantitative Überlegenheit über Plasmid-DNA unterstreichen zusätzlich die Effizienz der adenoviralen Vektoren; alle Ergebnisse werden dadurch bekräftigt, dass sie sich problemlos in den Kontext der Literatur einordnen lassen. Darüber hinaus enthalten die Vektoren alle Möglichkeiten der neuen vielversprechenden Technologie zur genetisch-chemischen Kapsidmodifikation. Alle Voraussetzungen - in vitro und in vivo - sind also erfüllt, um eine Vielzahl von Fragestellungen im Hinblick auf die Verbesserung von adenoviralen Vektoren für genetische Vakzinierung experimentell zu bearbeiten. Vorteile, vor allem im Hinblick auf das Sicherheitsprofil von Vektoren, kann zunächst die PEGylierung bieten. Diese Abschirmung des Kapsids soll verhindern, dass der Vektor seinen natürlichen Rezeptor CAR erkennt, der 115 von vielen verschiedenen Körperzellen 5 Diskussion (z.B. Hepatozyten) exprimiert wird. Diese Tatsache erschwert die Vorhersage über die Verteilung des Vektors im Organismus nach Injektion erheblich, denn selbst nach intramuskulärer Applikation ist es nicht auszuschließen, dass der Vektor in den Kreislauf und damit auch in andere Organe gelangt. Könnte also die Interaktion mit CAR unterbunden werden, wäre dies ein Fortschritt, was die Sicherheitsbedenken gegenüber viralen Vakzinierungsvektoren angeht. Des weiteren ist in diesem Zusammenhang die oftmals vorbestehende Immunität gegen das Adenovirus zu nennen. Diese kann in Form von neutralisierenden Antikörpern gegen das Kapsid den Erfolg der Immunisierung erheblich beeinträchtigen. Durch eine schützende PEG-Hülle könnten die Vektoren den Antikörpern entkommen und somit trotzdem eine Vakzinierung erlauben. Ein weiteres großes Feld eröffnet sich durch die Kopplungsmöglichkeit von Liganden an die zusätzlich eingeführten Cysteinreste. Der Auswahl der Liganden sind kaum Grenzen gesetzt und bei Bedarf kann zusätzlich PEGyliert werden, wodurch der Tropismus des Vektorpartikels nicht nur erweitert wird, sondern eine echte singuläre Spezifität erlangt. So könnte beispielsweise versucht werden, speziell antigenpräsentierende Zellen (z.B. dendritische Zellen), evtl. durch die Kopplung von Mannanen, gerichtet zu transduzieren, um dadurch eine effizientere Antigenprozessierung und –präsentation und daraus folgend eine höhere Immunantwort zu erzielen. Zur Stärkung der ausgelösten Immunantwort bietet sich auch die zusätzliche Kopplung von Antigenen auf die Virusoberfläche an. Entsprächen diese dem im Transgen kodierten Antigen, so könnten sie eine wünschenswerte adjuvante Wirkung haben und zusätzlich die Bildung der humoralen Antwort fördern, da die lösliche Form des Antigens von Beginn an vorläge. Das Ziel der Effizienzsteigerung durch Kopplung von Liganden ist die Auslösung der bestmöglichen Immunantwort durch eine möglichst niedrige Vektorpartikelzahl. Ein orientierender Schwellenwert für nicht-modifizierte Partikel wurde in der vorliegenden Arbeit bereits determiniert. Im Vergleich hierzu lässt sich die Effizienz der einzelnen Kopplungsexperimente messen. 116 5 Diskussion Zusätzlich wird zu jedem cysteinhaltigen Vektor derselbe nicht-cysteinhaltige Vektor bereitgestellt, wodurch in jedem Fall auch direkte Vergleiche zwischen den jeweiligen Immunantworten möglich sind. So besteht keine Abhängigkeit von tagesbedingten Schwankungen. Schließlich könnte die gerichtete Transduktion eines bestimmten Zelltyps auch genutzt werden, um dessen Rolle in der Generierung einer Immunantwort genauer zu evaluieren. Dies macht das Vektorsystem auch für immunologische Zwecke wertvoll. Ein Vergleich zwischen Vektoren, die unterschiedliche Transgene exprimieren, könnte Aufschluss über die Auswirkungen von Sezernierung bzw. intrazellulärem Verbleib der Transgenprodukte geben. Ergeben sich Unterschiede in Qualität und Quantität der induzierten Immunantwort, so könnte die Wahl des Transgens zusätzlich genutzt werden, um die Immunantwort in eine gewünschte Richtung zu beeinflussen. Erste Anhaltspunkte könnte ein Vergleich derselben Vektordosen innerhalb 117 gleicher Mausstämme geben. 6 Zusammenfassung 6 Zusammenfassung Genetische Vakzinierung ist ein zukunftsweisender Ansatz in der Bekämpfung von Infektionskrankheiten und Tumorerkrankungen. Unter den verschiedenen Gentransfersystemen, die derzeit getestet werden, spielt das Adenovirus aufgrund seiner guten Produzierbarkeit, des stabilen Genoms, das nicht in das der transduzierten Zellen integriert, und seiner relativen Ungefährlichkeit eine herausragende Rolle. Um limitierende Faktoren wie z.B. vorbestehende Immunität gegen den Vektor oder ungerichtete Transduktion zu umgehen, wurde in der Sektion Gentherapie der Universität Ulm eine Technologie für kombinierte genetische und chemische Kapsidmodifikationen der Vektoren entwickelt. Durch diese sollen ein Schutz der Vektoren vor neutralisierenden Antikörpern und eine spezifische Transduktion des Zielgewebes erreicht werden. Das Ziel der vorliegenden Arbeit war die Konstruktion und Charakterisierung verschiedener adenoviraler Vektoren zur Expression von Modellantigenen. Diese sollten neben der Transgenexpression die oben genannten genetisch-chemischen Kapsidmodifikationen erlauben und sich so für Immunisierungsversuche in vivo eignen, die eine detaillierte Untersuchung des Effektes dieser Kapsidmodifikationen auf die Eignung der Vektoren als genetische Vakzine gestatten. Im ersten Teil der vorliegenden Arbeit wurden drei Vektorpaare konstruiert, die sowohl die Möglichkeit bieten zwischen kapsidmodifizierten und nicht-kapsidmodifizierten Vektoren zu vergleichen als auch den Einfluss der Sezernierung bzw. des intrazellulären Verbleibs des transgenen Proteins auszuwerten. Es wurden die Modellantigene HBsAg (Hepatitis B Surface Antigen) und das Fusionsprotein T-OVA-EGFP (bestehend aus Teilen des „large tumor antigen“ des Simian Virus 40, des Ovalbumins und aus dem modifizierten grün fluoreszierenden Protein) als Transgene gewählt. Das gestattet durch international standardisierte Verfahren zur Quantifizierung der Immunantworten Vergleiche mit herkömmlichen Impfmethoden. Zur Erzeugung der adenoviralen Vektoren wurden Expressionskassetten für die Modellantigene in infektiöse adenovirale Plasmide kloniert und 118 6 Zusammenfassung die korrelierenden Vektoren amplifiziert und gereinigt. Es enstanden die zwei Vektorpaare AdHBsAg/Ad1CysHBsAg (adenovirale Erstgenerationsvektoren, die das HBsAg exprimieren; Cys: kapsidmodifiziert) und AdOVA/Ad1CysOVA (adenovirale Erstgenerationsvektoren, die das Fusionsprotein T-OVA-EGFP exprimieren) und zusätzlich ein adenovirales Kontrollvektorpaar ohne Transgen (Adempty/Ad1Cysempty). Anschließend erfolgten eine Bestimmung des Titers, die Prüfung der Vektorintegrität sowie der chemischen Qualität der Präparation und der Nachweis der funktionellen Aktivität in Transduktionsexperimenten in vitro. Im zweiten Teil der Arbeit wurden erste Versuche in vivo durchgeführt, um die Eignung der Vektoren zum Auslösen einer Immunantwort zu prüfen. Mit allen getesteten Vektoren konnte eine Immunantwort in Mäusen ausgelöst werden, deren Schwerpunkt auf den zytotoxischen T-Lymphozyten lag. Da dies ein Hauptziel der genetischen Vakzinierung darstellt, wird dadurch die Eignung der Vektoren für weiterführende Experimente bekräftigt. Es wurde ein Dosisbereich definiert, in dem sich die transgen-spezifische Immunantwort mit steigender Vektordosis erhöht (1108-11010 Vektorpartikel). Zusätzlich konnte eine Schwellendosis für die Immunisierung festgelegt werden, unter der keine T-Zell-Antwort mehr auslösbar war (1107 Vektorpartikel). Die subkutane und die intramuskuläre Injektionsroute wurden miteinander verglichen und als gleichwertig eingestuft. Im Vergleich zur Immunisierung mit Plasmid-DNA gab es deutliche Hinweise für eine höhere Effizienz der Vektoren (in den gezeigten Experimenten ca. drei- bis siebenfach). Für erste Versuche mit chemisch modifizierten Vektoren wurden AdHBsAg und AdOVA mit einer Polyethylenglykol-Hülle versehen (= PEGyliert). Die PEGylierten Vektoren zeigten in vitro eine stark reduzierte Infektiosität (< 5%). Nach Injektion in vivo ergab sich jedoch eine überraschend hohe zelluläre Immunantwort, die nur ca. 50% unter der der nicht-PEGylierten Vergleichsvektoren lag. Die konstruierten Vektoren bilden die Basis für weitergehende Versuche, in denen die Wirkung chemischer Kapsidmodifikation mit Liganden und PEG untersucht werden sollen. 119 Literatur Literaturverzeichnis [1] Basak SK, Kiertscher SM, Harui A, Roth MD: Modifying Adenoviral vectors for use as gene-based cancer vaccines. Viral Immunol 17: 182-196 (2004) [2] Belousova N, Korokhov N, Krendelshchikova V, Simonenko V, Mikheeva G, Triozzi PL, Aldrich WA, Banerjee PT, Gillies SD, Curiel DT, Krasnykh V: Genetically targeted adenovirus vector directed to CD40-expressing cells. J Virol 77: 11367-11377 (2003) [3] Casimiro DR, Chen L, Fu T-M, Evans RK, Caulfield MJ, Davies M-E, Tang A, Chen M, Huang L, Harris V, Freed DC, Wilson KA, Dubey S, Zhu D-M, Nawrocki D, Mach H, Troutman R, Isopi L, Williams D, Hurni W, Xu Z, Smith JG, Wang S, Liu X, Guan L, Long R, Trigona W, Heidecker GJ, Perry HC, Persaud N, Toner TJ, Su Q, Liang X, Youil R, Chastain M, Bett AJ, Volkin DB, Emini EA, Shiver JW: Comparative immunogenicity in rhesus monkeys of DNA plasmid, recombinant vaccinia virus, and replication-defective Adenovirus vectors expressing a human immunodeficiency virus type 1 gag gene. J Virol 77: 6305-6313 (2003) [4] Casimiro DR, Tang A, Chen L, Fu T-M, Evans RK, Davies M-E, Freed DC, Hurni W, Aste-Amezaga JM, Guan L, Long R, Huang L, Harris V, Nawrocki DK, Mach, Troutman RD, Isopi LA, Murthy KK, Rice K, Wilson KA, Volkin DB, Emini EA, Shiver JW: Vaccine-induced immunity in baboons by using DNA and replicationincompetent Adenovirus type 5 vectors expressing a human immunodeficiency virus type 1 gag gene. J Virol 77: 7663-7668 (2003) [5] Casimiro DR, Bett AJ, Fu T-M, Davies M-E, Tang A, Wilson KA, Chen M, Long R, McKelvey T, Chastain M, Gurunathan S, Tartaglia J, Emini EA, Shiver J: Heterologous human immunodeficiency virus type 1 priming-boosting immunization strategies involving replication-defective adenovirus and poxvirus vaccine vectors. J Virol 78: 11434-11438 (2004) 120 Literatur [6] Chen P, Kovesdi I, Bruder JT: Effective repeat administration with adenovirus vectors to the muscle. Gene Ther 7: 587-595 (2000) [7] Clark KR, Johnson PR: Gene delivery of vaccines for infectious disease. Curr Opin Mol Ther 3: 375-384 (2001) [8] Croyle MA, Le HT, Linse KD, Cerullo V, Toietta G, Beaudet A, Pastore L: PEGylated helper-dependent adenoviral vectors: highly efficient vectors with an enhanced safety profile. Gene Ther 12: 579-587 (2005) [9] Fontana L, Nuzzo M, Urbanelli L, Monaci P: General strategy for broadening Adenovirus tropism. J Virol 77: 11094-11104 (2003) [10] Ganem D, Hollinger FB: Hepadnaviridae. In: Fields BN, Knipe DM, Howley PM, Chanock RM, Melnick JL, Monath TP, Roizman B, Straus SE (Hrsg) Fields Virology, Bd 2, 3. Aufl, Lippincott-Raven, Philadelphia, New York, S. 2703-2808 (1996) [11] Huovila A-PJ, Eder AM, Fuller SD: Hepatitis B surface antigen assembles in a post-ER, pre-Golgi compartment. J Cell Biol 118: 1305-1320 (1992) [12] Imperiale MJ, Kochanek S: Adenovirus vectors: Biology, Design and Production. Curr Top in Microbiol Immunol 273: 335-357 (2004) [13] Kochanek S, Clemens PR, Mitani K, Chen HH, Chan S, Caskey CT: A new adenoviral vector: Replacement of all viral coding sequences with 28 kb of DNA independently expressing both full-length dystrophin and beta-galactosidase. Proc Natl Acad Sci USA 93: 5731-5736 (1996) [14] Kreppel F, Biermann V, Kochanek S, Schiedner G: A DNA-based method to assay total and infectious particle contents and helper virus contamination in high-capacity adenoviral vector preparations. Hum Gene Ther 13: 1151-1156 (2002) [15] Kreppel F, Gackowski J, Schmidt E, Kochanek S: Combined genetic and chemical capsid modifications enable flexible and efficient de- and retargeting of Adenovirus vectors. Mol Ther 12: 107-117 (2005) [16] Kreppel F: (unveröffentlichte Befunde) [17] Kreppel F: (2005 persönliche Mitteilung) 121 Literatur [18] Markesich DC, Sawai ET, Butel JS, Graham DY: Investigations on etiology of Crohn’s disease. Humoral immune response to stress (heat shock) proteins. Dig Dis Sci 36: 454460 (1991) [19] Mascola JR, Sambor A, Beaudry K, Santra S, Welcher B, Louder MK, VanCott TC, Huang Y, Chakrabarti BK, Kong W-P, Yang Z-Y, Xu L, Montefiori DC, Nabel GJ, Letvin NL: Neutralizing antibodies elicited by immunization of monkeys with DNA plasmids and recombinant adenoviral vectors expressing human immunodeficiency virus type 1 proteins. J Virol 79: 771-779 (2005) [20] McKelvey T, Tang A, Bett AJ, Casimiro DR, Chastain M: T-cell response to adenovirus hexon and DNA-binding protein in mice. Gene Ther 11: 791-796 (2004) [21] Mittereder N, March KL, Trapnell BC: Evaluation of the concentration and bioactivity of adenovirus vectors for gene therapy. J Virol 70: 7489-7509 (1996) [22] Molinier-Frenkel V, Lengagne R, Gaden F, Hong SS, Choppin J, Gahery-Segard H, Boulanger P, Guillet JG: Adenovirus hexon protein is a potent adjuvant for activation of a cellular immune response. J Virol 76: 127-135 (2002) [23] O’Riordan CR, Lachapelle A, Delgado C, Parkes V, Wadsworth SC, Smith AE, Francis GE: PEGylation of adenovirus with retention of infectivity and protection from neutralizing antibody in vitro and in vivo. Hum Gene Ther 10: 1349-1358 (1999) [24] Patzer EJ, Nakamura GR, Yaffe A: Intracellular transport and secretion of hepatitis B surface antigen in mammalian cells. J Virol 51: 346-353 (1984) [25] Pereboev AV, Nagle JM, Shakhmatov MA, Triozzi PL, Matthews QL, Kawakami Y, Curiel DT, Blackwell JL: Enhanced gene transfer to mouse dendritic cells using Adenoviral vectors coated with a novel adapter molecule. Mol Ther 9: 712-720 (2004) [26] Peterson DL: Isolation and characterization of the major protein and glycoprotein of hepatitis B surface antigen. J Biol Chem 256: 6975-6983 (1981) [27] Reimann J, Schirmbeck R: DNA vaccines expressing antigens with a stress proteincapturing domain display enhanced immunogenicity. Immunol Rev 199: 54-67 (2004) [28] Reyes-Sandoval A, Fitzgerald JC, Grant R, Roy S, Xiang ZQ, Li Y, Gao GP, Wilson JM, Ertl HCJ: Human immunodeficiency virus type 1-specific immune responses in primates 122 Literatur upon sequential immunization with adenoviral vaccine carriers of human and simian serotypes. J Virol 78: 7392-7399 (2004) [29] Rocha CD, Caetano BC, Machado AV, Bruna-Romero O: Recombinant viruses as tools to induce protective cellular immunity against infectious diseases. Int Microbiol 7: 83-94 (2004) [30] Schiedner G, Hertel S, Kochanek S: Efficient transformation of primary human amniocytes by E1 functions of Ad5: Generation of new cell lines for Adenoviral vector production. Hum Gene Ther 11: 2105-2116 (2000) [31] Schirmbeck R, Reimann J: Peptide transporter-independent stress protein-mediated endosomal processing of endogenous protein antigens for major histocompatibility complex class I presentation. Eur J Immunol 24: 1478-1486 (1994) [32] Schirmbeck R, Reimann J: Revealing the potential of DNA-based vaccination: Lessons learned from the hepatitis B virus surface antigen. Biol Chem 382: 543-552 (2001) [33] Schirmbeck R: (2005 persönliche Mitteilung) [34] Shenk T, Horwitz MS. Adenoviridae. In: Fields BN, Knipe DM, Howley PM, Chanock RM, Melnick JL, Monath TP, Roizman B, Straus SE (Hrsg). Fields Virology, Bd 2, 3. Aufl, Lippincott-Raven, Philadelphia, New York, S. 2111-2172 (1996) [35] Shiver JW, Fu T-M, Chen L, Casimiro DR, Davies M-E, Evans RK, Zhang Z-Q, Simon AJ, Trigona WL, Dubey SA, Huang L, Harris VA, Long RS, Liang X, Handt L, Schleif WA, Zhu L, Freed DC, Persaud NV, Guan L, Punt KS, Tang A, Chen M, Wilson KA, Collins KB, Heidecker GJ, Fernandez VR, Perry HC, Joyce JG, Grimm KM, Cook JC, Keller PM, Kresock DS, Mach H, Troutman RD, Isopi LA, Williams DM, Xu Z, Bohannon KE, Volkin DB, Montefiori DC, Miura A, Krivulka GR, Lifton MA, Kuroda MJ, Schmitz JE, Letvin NL, Caulfield MJ, Bett AJ, Youil R, Kaslow DC, Emini EA: Replication-incompetent adenoviral vaccine vector elicits effective anti- immunodeficiency-virus immunity. Nature 415: 331-335 (2002) [36] Stevenson FK, Ottensmeier CH, Johnson P, Zhu D, Buchan SL, McCann KJ, Roddick JS, King AT, McNicholl F, Savelyeva N, Rice J: DNA vaccines to attack cancer. Proc Natl Acad Sci USA 101 Suppl 2: 14646-14652 (2004) 123 Literatur [37] Stober D, Trobonjaca Z, Reimann J, Schirmbeck R: Dendritic cells pulsed with exogenous hepatitis B surface antigen particles efficiently present epitopes to MHC class I-restricted cytotoxic T cells. Eur J Immunol 32: 1099-1108 (2002) [38] Sumida SM, Truitt DM, Kishko MG, Arthur JC, Jackson SS, Gorgone DA, Lifton MA, Koudstaal M, Pau MG, Kostense S, Havenga MJE, Goudsmit J, Letvin NL, Barouch DH: Neutralizing antibodies and CD8+ T lymphocytes both contribute to immunity to adenovirus serotype 5 vaccine vectors. J Virol 78: 2666-2673 (2004) [39] Tatsis N, Ertl HCJ: Adenoviruses as vaccine vectors. Mol Ther 10: 616-629 (2004) [40] Vogels R, Zuijdgeest D, van Rijnsoever R, Hartkoorn E, Damen I, de Béthune M-P, Kostense S, Penders G, Helmus N, Koudstaal W, Cecchini M, Wetterwald A, Sprangers M, Lemckert A, Ophorst O, Koel B, van Meerendonk M, Quax P, Panitti L, Grimbergen J, Bout A, Goudsmit J, Havenga M: Replication-deficient human Adenovirus type 35 vectors for gene transfer and vaccination: Efficient human cell infection and bypass of preexisting Adenovirus immunity. J Virol 77: 8263-8271 (2003) [41] Volpers C, Kochanek S: Adenoviral vectors for gene transfer and therapy. J Gene Med 6 Suppl 1: 164-171 (2004) [42] Worgall S, Busch A, Rivara M, Bonnyay D, Leopold PL, Merritt R, Hackett NR, Rovelink PW, Bruder JT, Wickham TJ, Kovesdi I, Crystal RG: Modification to the capsid of the Adenovirus vector that enhances dendritic cell infection and transgenespecific cellular immune responses. J Virol 78: 2572-2580 (2004) [43] Yang Y, Haecker SE, Su Q, Wilson JM: Immunology of gene therapy with adenoviral vectors in mouse skeletal muscle. Hum Mol Genet 5: 1703-1712 (1996) [44] Yang Z-Y, Wyatt LS, Kong W-P, Moodie Z, Moss B, Nabel GJ: Overcoming immunity to a viral vaccine by DNA priming before vector boosting. J Virol 77: 799-803 (2003) [45] Zhang L, Tang Y, Akbulut H, Zelterman D, Linton P-J, Deisseroth AB: An adenoviral vector cancer vaccine that delivers a tumor-associated antigen/CD40-ligand fusion protein to dendritic cells. Proc Natl Acad Sci 100: 15101-15106 (2003) 124 Danksagungen Mein herzlichster Dank gilt: - Prof. Dr. Stefan Kochanek für die Möglichkeit, diese Arbeit in seinem Labor anfertigen zu dürfen, für sein fortwährendes Interesse und seine Unterstützung. - Prof. Dr. Thomas Mertens für die bereitwillige Begutachtung der Dissertationsschrift. - Florian Kreppel, dem besten Betreuer der Welt, für die intensive Unterstützung, für viel Zeit, Geduld und immer ein offenes Ohr. - Judith Kurdum und Erika Schmidt für die Einführung in die Laborarbeit, geduldiges Erklären und tatkräftige Hilfe. - Andreas Wortmann für die große Hilfe bei der Durchführung und Auswertung der Tierexperimente. - der ganzen Sektion Gentherapie für die freundliche Aufnahme, die gute Zusammenarbeit und das gute Arbeitsklima. - Prof. Dr. Reinhold Schirmbeck für die große Unterstützung und die Beratung bei den Tierexperimenten. - Petra Riedl für die Hilfe bei der Immunpräzipitation. - Gabi Breymaier für das überaus gründliche Lektorat. - der DFG, die mir durch ein Stipendium ein Jahr intensive Forschung ermöglichte. - Jürgen Ebert für seine Liebe und sehr viel Verständnis. - meiner Familie für ihr intensives Teilnehmen an meiner Arbeit, für Ermutigung und Unterstützung. Lebenslauf Sabine Vöhringer Jörg-Syrlin-Str. 130 89081 Ulm Staatsangehörigkeit : deutsch 15.12.1981 : geboren in Reutlingen 1988-1992 : Besuch der Grundschule in Ohmenhausen 1992-2001 : Besuch des Johannes-Kepler-Gymnasiums in Reutlingen Juni 2001 : Erwerb der Allgemeinen Hochschulreife 2001-2008 : Studium der Humanmedizin an der Universität Ulm seit 2003 : Stipendiatin des Cusanuswerkes Sept 2003 : Ärztliche Vorprüfung Okt 2004 –Sept 2005 : Praktische Arbeit der Dissertation Jan 2008 : Promotionskolloquium Nov 2008 : 2. Ärztliche Prüfung und Erlangung der Approbation