Anleitung-F1_Bioinformatik
Werbung

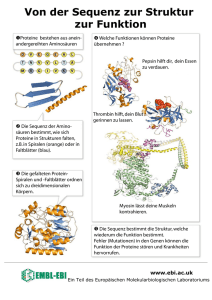
F1-Praktikum "Molekulare Zoologie" Kursteil: Bioinformatik (Thorsten Burmester) Molekulare Sequenzanalyse von Hämocyanin 1. EINLEITUNG 1.1 Hämocyanin Respiratorische Proteine dienen der Versorgung des Organismus mit Sauerstoff. Im Tierreich sind drei Typen respiratorischer Proteine verbreitet: Hämoglobin, Hämerythrin und Hämocyanin. Hämocyanine sind große kupferhaltige Proteine, die den Sauerstoff in der Hämolymphe vieler Arthropoden und Mollusken transportieren. Die Hämocyanine dieser beiden Tierstämme unterscheiden sich jedoch fundamental in Sequenz und Struktur, weshalb eine konvergente Evolution aus unterschiedlichen Typen von Kupferproteinen zu vermuten ist. Arthropoden-Hämocyanine bilden stets Hexamere oder Oligohexamere (1 bis 8 x 6-Struktur) aus ähnlichen oder identischen Untereinheiten (Abb. 1). Abb. 1. Quartärstruktur der Arthropodenhämocyanine: (a) 2 6 Hämocyanin vieler dekapoden Crustacea (z.B. Homarus americanus), (b) 2 6 Hämocyanin vieler Spinnen (z.B. Cupiennius salei), (c) 4 6 Hämocyanin einiger Garnelen (z.B. Callianassa californiensis), (d) 4 6 Hämocyanin vieler Arachniden (z.B. Eurypelma californicum), (e) 2 6 Hämocyanin des Fangschreckenkrebses Squilla mantis, (f) 6 6 Hämocyanin der Myriapoden (z.B. Scutigera coleoptrata), (g) 8 6 Hämocyanin von Limulus polyphemus. Jede Untereinheit umfasst etwa 620 bis 660 Aminosäuren (entspricht etwa 70 – 80 kDa) und kann ein O2-Molekül mittels zweier Kupferionen (Cu+) binden, die jeweils durch drei Histidine der Proteinkette koordiniert werden (CuA- und CuB-Bindungsstelle) (Abb. 2). Aufgrund dieser Struktur des aktiven Zentrums werden die Hämocyanine den so genannten "Typ 3"Kupferproteine zugerechnet. Zu dieser Klasse von Metallo-Proteinen gehören ferner die bereits genannten Mollusken-Hämocyanine, sowie die Tyrosinasen und Catecholoxidasen (Sammelbegriff: Phenoloxidasen) vieler Tierstämme. Abb. 2. Schematisierte Struktur eines binukleären Typ 3-Kupferbindungszentrum. Strukturanalysen zeigten, dass die Hämocyanin-Untereinheiten etwa nierenförmig sind und aus drei Domänen bestehen (Abb. 3). Die N-terminale erste Domäne (~180 Aminosäuren) besteht aus einem -helicalen Bündel und schützt das aktive Zentrum. Domäne 2 (~220 Aminosäuren) besteht ebenfalls vor allem aus α-Helices. Sie ist am stärksten konserviert und trägt das aktive Zentrum mit den beiden Kupferionen. Domäne 3 (~260 Aminosäuren) enthält mehrere β-Faltblattstrukturen, die ein siebensträngiges antiparalleles "Beta-Barrel“ bilden. Obwohl Arthropoden-Hämocyanine stets Hexamere oder Oligohexamere bilden (Abb. 1), ist die Untereinheitenzusammensetzung sehr variabel. Kontakte zwischen den Untereinheiten erfolgen in der Regel durch nicht-kovalente Bindungen. Abb. 3. 3D-Struktur einer Hämocyaninuntereinheit der Languste P. interruptus. Die Domäne 1 ist grün, die Domäne 2 rot, die Domäne 3 blau. Die beiden Kupferatome (Pfeil) sind dunkelblau eingefärbt. 1.2 Die Hämocyanin-Superfamilie In den letzten 10 Jahren konnte gezeigt werden, dass bestimmte Proteine signifikante Sequenzübereinstimmungen mit den Hämocyaninen aufweisen, jedoch andere Funktionen übernehmen. Gemeinsam werden sie als "Hämocyanin-Superfamilie" zusammengefasst, die neben den Hämocyaninen, auch Phenoloxidasen, Pseudohämocyanine, Hexamerine und Hexamerinrezeptoren umfasst. Phenoloxidasen sind sauerstoffumsetzende Enzyme des Melaninstoffwechsels und an der Sklerotisierung der Kutikula, der humoralen Immunantwort und der Wundheilung beteiligt. Wie Hämocyanine haben sie ein Typ 3-Kupferzentrum. Die anderen Hämocyanin-ähnlichen Proteine, d.h., die Pseudohämocyanine einiger dekapoder Krebse und Hexamerine der Insekten, haben die Kupferbindungsstellen verloren. Sie dienen wohl v.a. als Speicherproteine für nahrungsarme Zeiten, obwohl den Hexamerinen auch andere Funktionen zugeschrieben werden. Ebenfalls zur Hämocyanin-Superfamilie gehören Hexamerinrezeptoren, die bislang nur in Fliegen (Diptera) gefunden wurden. 1.3 Die Hämocyanine der Crustacea Zwar wurden inzwischen in Vertretern aller Unterstämme der Arthropoden (Onychophora, Cherlicerata, Crustacea, Myriapoda und Insecta) Hämocyanine gefunden, doch liegen umfangreiche Untersuchungen bislang nur über Cheliceraten (Spinnentiere) und Crustaceen (Krebse) vor. Innerhalb der Krebse scheint das Vorkommen von Hämocyanin auf die Klasse der Malacostraca beschränkt zu sein, während die "Entomostraca" (ein wahrscheinlich paraphyletisches Taxon) über entweder keine respiratorischen Proteine, oder aber über Hämoglobin (z.B. Daphnia) verfügt. Die größte und bekannteste Gruppe der Malacostraca sind die Decapoda (Zehnfußkrebse), zu denen auch Astacus gehört. Die Hämocyanine der Decapoda sind entweder Hexamere (1 x 6) oder Di-Hexamere (2 x 6) aus bis zu sechs verschiedenen Untereinheiten. Diese lassen sich wiederum in drei Typen einteilen, die nach Markl (1986) , and genannt werden. Die Untereinheitenzusammensetzung unterscheidet sich je nach Art, Entwicklungsstadium oder physiologischem Zustand. 2. ABLAUF DES KURSES 2.1 Ziel Zum Verständnis der Proteinfunktion ist die Kenntnis von Struktur und Evolution eine wichtige Voraussetzung. Hierfür muss die Proteinsequenz ermittelt werden. Dies macht man heute gewöhnlich über cDNA-Sequenzen, die anschließend in Protein übersetzt werden. Sie sollen in diesem Kursteil lernen, wie Sie die bei der Sequenzierung erhaltene Information lesen, auswerten und interpretieren. Hierfür wollen wir uns verschiedener Programme und öffentlich zugänglicher Datenbanken bedienen. 2.2 Zeitplan Informieren Sie sich vor Beginn des Kursteils in einem Lehrbuch kurz über die Systematik der Arthropoden im Allgemeinen und über die der Crustacea im Speziellen. Informieren Sie sich – falls nötig – über folgende Begriffe und Techniken: - PCR (Polymerasenkettenreaktion) - DNA-Sequenzierung nach der Sanger-Kettenabbruchmethode - Restriktionsenzym - Molekulargewicht - isoelektrischer Punkt Tag 1 (Dienstag, 12.3.2005): Auswertung von Sequenzierungs-Ergebnissen Datenbankanalysen Untersuchung der Primärsequenz Molekulare Phylogenie Tag 2 (Mittwoch, 13.3.2005): Molekulare Phylogenie (Fortsetzung) Auswertung der Ergebnisse Vorstellung der Ergebnisse im Seminar 3. ANLEITUNG 3.1 Vorbemerkung Alle notwendigen Programme und Dateien finden Sie unter: www.staff.uni-mainz.de/~burmeste/F1 Legen Sie sich auf Ihrem Laufwerk "U:\" ein eigenes Verzeichnis "Zoologie" an. Kopieren Sie die bereit gestellten Daten in dieses Verzeichnis. Bitte verwenden Sie während des Kurses dieses Verzeichnis, und nur dieses Verzeichnis, als Speicherort für Ihre Dateien. 3.2 Analyse der eines Hämocyanin-Klons von Astacus Die cDNA kann über verschiedene Methoden gewonnen werden (AntikörperScreening, DNA-Sonden-Screening, PCR). Diese wird in einen geeigneten Vektor (Plasmid; hier pBluescript SK-) kloniert und kann mittels Vektor-spezifischer Primer (kurze, 17 – 25 Basenpaare lange Oligonukleotide, die an die Sequenz des Vektors binden) sequenziert werden. Üblicherweise sequenziert man heute nicht mehr selbst, sondern überlässt dies einem kommerziellen Unternehmen. Das Plasmid, welches die cDNA einer Hämocyanin-Untereinheit von Astacus enthält, wurde bereits in der Arbeitsgruppe mit den beiden Standardprimern für den Vektor (T3 und T7) von beiden Seiten sequenziert. Sie erhalten zwei Sequenz-Dateien, wie sie von der Firma per E-mail zugeschickt wurden. Durchführung: • Öffnen Sie die Sequenz-Datei mit dem Programm "Chromas". Schauen Sie sich diese Datei an und suchen Sie nach "N"s. Was ist dort passiert? • Welche der beiden Sequenzen entspricht dem 5' bzw. 3'-Ende? Wo endet der Vektor, wo beginnt die cDNA? Suchen sie die Schnittstellen der beiden Restriktionsenzyme EcoR1 (GAATTC) und XhoI (CTCGAG). • Suchen Sie in der 3'-Sequenz die Polyadenylierungsstelle (AATAAA) Nun wollen Sie wissen, ob die sequenzierte cDNA tatsächlich für Hämocyanin kodiert. Hierzu sollen die Datenbanken der bereits vorhandenen Sequenzen mit der eigenen Sequenz durchsucht werden. Es stehen drei Datenbanken zur Auswahl: 1. NCBI-BLAST http://www.ncbi.nlm.nih.gov/BLAST/ 2. EBI-BLAST: http://www.ebi.ac.uk/Tools/similarity.html 3. BLAST-Japan: http://blast.genome.ad.jp/ Kopieren Sie die cDNA (aus "Astacus_Hc_T3.dat") in die entsprechende Dialogbox. Wählen Sie die Option "blastx" (wird im Kurs erklärt). Handelt es sich tatsächlich um Hämocyanin? Mit welchem Protein ist die eigene Sequenz am nächsten verwandt? Ist die eigene Sequenz vollständig? Führen Sie anschließend die gleichen Schritte mit der Sequenz aus "Astacus_Hc_T7.dat" durch. 3.2 Sequenzdatenanalyse des Hämocyanins von Pacifastacus leniusculus Leider ist es uns bislang noch nicht gelungen, die cDNA-Sequenz einer HämocyaninUntereinheit von Astacus vollständig zu klonieren und zu sequenzieren Sie erhalten daher die vollständige Sequenz der Hämocyanin-cDNA der verwandten Spezies Pacifastacus leniusculus. Ihre Aufgabe ist es zuerst, die cDNA-Sequenz in ein Protein zu übersetzen, das Molekulargewicht dieses Proteins zu bestimmen und den isoelektrischen Punkt zu errechnen. Durchführung: • Öffnen Sie die bereitgestellte Textdatei mit der Hämocyanin-Sequenz (Pacifastacus Hämocyanin.txt) mit einem Editor (z.B. Word). Zur Übersetzung der cDNA in Protein stehen verschiedene Programme zur Verfügung. Wir verwenden eine Netz-basierte Applikation: http://www.expasy.org/tools/dna.html • Kopieren Sie die DNA-Sequenz wiederum in die dafür vorgesehene Dialogbox und und starten sie die das Programm ("Translate Sequence"). • Nun erhalten Sie die in allen sechs möglichen Leserastern translatierte DNA-Sequenz. Wählen Sie das geeignete Leseraster. Woran erkennen Sie, welches Leseraster das richtige ist? Das so erhaltene Protein kopieren Sie und speichern Sie dieses in Ihrem Verzeichnis als Textdatei ab. • Bestimmen Sie nun das Molekulargewicht und den theoretischen isoelektrischen Punkt mittels eines weiteren Web-basierten Applikation: http://www.expasy.ch/tools/pi_tool.html 3.3 Sequenzalignments Zur phylogentischen Analyse müssen Sie geeignete Vergleichssequenzen auswählen. Dazu können Sie wiederum mit den BLAST-Programmen die Proteindatenbanken durchsuchen (diesmal Option "blastp", d.h. Vergleich eines Proteins mit anderen Proteinen): 1. NCBI-BLAST: http://www.ncbi.nlm.nih.gov/BLAST/ 2. EBI-BLAST: http://www.ebi.ac.uk/blast2/ 3. BLAST-Japan: http://blast.genome.ad.jp/ • Als nächstes sollen einige ausgewählte Proteine mit dem Pacifastacus-Hämocyanin verglichen werden. • Öffnen Sie zunächst das Programm "GENEDOC". Wählen Sie aus den Datenbanken (NCBI etc; siehe oben) ca. 10 verschiedene Hämocyanine aus. Die Auswahl bleibt Ihnen überlassen. • Kopieren Sie die Aminosäuresequenzen mit Hilfer der vorgesehenen Dialogbox (Knopf "S" -> "import" -> "input") in GENEDOC. Verwenden Sie die in den Datenbanken vorgegebenen Namen bzw. geeignete Abkürzungen. Kopieren Sie ihre eigene Sequenz in GENEDOC. • Wenn Sie fertig sind, speichern Sie die Datei in Ihrem Verzeichnis unter "Hc.msf". • Exportieren Sie die Datei im CLUSTAL-Format. (Knopf "file" -> "export" -> "Clustal (aln)". Benennen Sie Ihre Datei "Hc.aln". • Nach dem Abspeichern öffnen Sie das Programm "CLUSTALX" und laden die Datei "Hc.aln" (Menü "File" -> "Load Sequences"). Nun "alignen" Sie die Sequenzen. D.h., das Programm versucht die Sequenzen so aneinanderzulegen, daß sie optimal übereinstimmen. Dafür müssen in einige Sequenzen Lücken bzw. Insertionen eingefügt werden. Sie können hierfür die Standardeinstellungen von CLUSTAL verwenden: Menü: "Alignment" -> "Do Complete Alignment". Nach Bestätigung der Dialogbox ("OK") nimmt der Sequenzvergleich einige Sekunden in Anspruch. • Was erkennen Sie an diesem Alignment? Was hat das Programm mit den Sequenzen, im Vergleich zu den Ausgangsdaten, gemacht? 3.4 Molekulare Phylogenie der Hämocyanine ClustalX bietet die Möglichkeit einer einfachen phylogenetischen Analyse. Diese soll jedoch für einen ersten Überblick dienen, zur genauen Untersuchung der phylogenetischen Verwandtschaftsverhältnisse sind i.d.R. bessere Methoden und Programme notwendig, die jedoch im Rahmen dieses Kurses nicht weiter betrachtet werden können. Hierfür wählen Sie in ClustalX unter dem Menü-Punkt "Trees" zunächst die Option "Correct for multiple substitutions". Anschließend führen Sie mit "Draw N-J Tree" (ebenfalls unter dem Menü "Trees") die Stammbaumanalyse durch. Öffnen Sie den Stammbaum mit dem Program "TreeView" und betrachten Sie ihn. Welche Schlüsse können Sie ziehen?